Vortrag von Philipp Nerke und Bruno Voigt
|
|
|
- Gerd Rothbauer
- vor 6 Jahren
- Abrufe
Transkript
1 Vortrag von Philipp Nerke und Bruno Voigt
2 Was war bekannt? Wirkung von Auxin Streckungswachstum Apicaldominanz Gravitropismus Laterales Wurzelwachstum Bekannte Gene der Auxin-Regulation AXR1 AXR4 AUX1 Protein, Ähnlichkeit mit Ubiquitin-activating enzyme (E1) Nicht weiter untersucht Membranprotein mit Ähnlichkeit zu Aminosäure-Permeasen SAR1 Epistatisch über AXR1, AXR4 ARF1 AUX/IAA AuxRE
3
4 Vorheriges Paper von Ruegger et al.: Screening nach Mutanten mit Resistenz gegenüber Auxin Transport Inhibitoren Auxin-transport inhibitors NPA (Naphthylphtalamic acid): CPD (2-Carboxyphenyl-3-phenylpropane-1,2-dione): Effekte: 1. eingeschränktes laterales Wurzelwachstum 2. gestörter Gravitropismus 3. Inhibierung Wurzelwachstum, Anschwellen der Wurzelspitze
5 TIR1 Mutantenscreen Screening Mutagenese EMS -NPA (Kontrolle) + NPA +NPA 16 TIR Mutanten gefunden Ziel: Identifizierung eines weiteren Gens im Auxin Pathway TRANSPORT INHIBITOR RESPONSE 1 (TIR1)
6 TIR1 Mutation Dominanz? Analyse der genetischen Basis für die Resistenz gegenüber CPD/NPA Beobachtung: 3 Phänotypen Vermutung: WT, heterozygot, homozygot tir1 (on 5 µm CPD) P tir1/tir1 x +/+ F 1 tir1/+ F 2 tir1/tir1 tir1/+ +/+ 1 : 2 : 1 Semidominanter Erbgang?
7 TIR1 Mutation Semidominanz Vergleich von Populationen homo- und heterozygoter TIR1 Mutanten Homozygote Mutanten weisen stärkste Resistenz auf Resistenzniveau heterozygoter Mutanten liegt zwischen dem homozygoter Mutanten und dem Wildtyp tir1-1 und tir1-3 ungefähr gleich stark, tir1-7 etwas schwächer Semidominanz
8 TIR1 Mutation Semidominanz Auxin Response oder Transport? Wichtigste Auswirkungen von CPD/NPA: Inhibierung Wurzelwachstum Anschwellen der Wurzelspitze Vermutete Ursache: Akkumulation von Auxin in dieser Region, durch Inhibierung des Auxin Transports weg von der Wurzelspitze Wirkung auf Auxin Transport oder Auxin Response?
9 TIR1 Mutation Semidominanz Auxin Response oder Transport? Einfluss der TIR1 Mutation auf die Auxin Response Wildtyp tir1-1 Mutante weist in Gegenwart von NPA stärkeres Wachstum als Wildtyp auf Mutanten sind resistenter gegenüber wachstumsinhibierenden Auxin- Konzentrationen Vermutung: TIR1 in Auxin Response involviert
10 TIR1 Mutation Semidominanz Auxin Response oder Transport? Auxin-transport assay Quelle: ( ) Modifiziert nach Nerke/Voigt
11 TIR1 Mutation Semidominanz Auxin Response oder Transport? Auxin-transport assay Wildtyp tir1-1 polarer Auxintransport ist in tir1-1 unverändert Auxin Response cpm = counts per minute
12 TIR1 Mutation Semidominanz Auxin Response Zellproliferation durch Auxin-transport Inhibitoren in tir1-1 Wildtyp Wurzeln zeigen erhöhte Proliferation tir1-1 Mutanten zeigen nur geringe Veränderung Auxin Response vermindert in tir1-1
13 TIR1 Mutation Semidominanz Auxin Response Auxinbehandlung induziert Bildung und Wachstum lateraler Wurzeln WT tir1-1 Auxin induziert Wurzelbildung in WT und tir1-1 Antwort von tir1-1 geringer Anzahl Lateralwurzeln steigt auch bei tir1-1 (entgegen der Erwartung) Behandlung von Wurzelsegmenten 5 Tage alter Keimlinge mit verschiedenen Konzentrationen IAA WT tir Tage alte Keimlinge auf 0,5 mm 2,4-D TIR1 Gen ist an Lateralwurzelbildung beteiligt Andere Vermutung: anderes Protein ist redundant mit Funktion von TIR1
14 TIR1 Mutation Semidominanz Auxin Response Temperaturabhängigkeit des Hypokotylwachstums Verlängerung des Hypokotyls bei erhöhter Temperatur primär durch Verlängerung der Epidermiszellen Hypokotyl bei tir1-1 nur unerheblich verlängert gleiche Beobachtung für iaalys-transgene Pflanzen (verminderte IAA-Konzentration) bei Gibberellinsynthese- und Ethylenantwort- Mutanten normale Reaktion Hypokotylwachstum bei erhöhter Temperatur auxinabhängig 9 Tage alte Keimlinge von WT und tir1-1: 4,5-fache Verlängerung bei WT 2,6-fache Verlängerung bei tir1-1 TIR1 in Hypokotylwachstum verwickelt
15 TIR1 Mutation Semidominanz Auxin Response Interaktion AXR1-TIR1? Interaktion zwischen AXR1 und TIR1 AXR1 benötigt für Auxin Response Generierung von homozygoten Pflanzen für axr1-12 und tir1-1, testen auf Auxin Response wt tir1-1 axr1-12 tir1-1 axr1-12 axr1-12 tir1-1 Keimlinge resistenter gegen 2,4-D als axr1-12 Keimlinge tir1-1 alleine bringt bei diesen Auxinkonzentrationen keine Resistenz hervor Effekt ist synergetisch
16 TIR1 Mutation Semidominanz Auxin Response Interaktion AXR1-TIR1 Interaktion zwischen AXR1 und TIR1 Morphologie der Doppelmutanten wt tir1-1 axr1-12 tir1-1 axr1-12 tir1-1 Rosette und Infloreszenz wie bei Wildtyp tir1-1: kleiner, etwas mehr sekundäre Infloreszenzen (Einfluss auf Apikaldominanz?) nach 12 Tagen auf 1µM 2,4-D axr1-12 und tir1-1 axr1-12: kleiner und eingeschränkte Apikaldominanz Funktion von TIR1 in aerial structures? 35 Tage nach Keimung TIR1 involviert in AXR1- vermittelten Prozessen?
17 TIR1 Mutation Semidominanz Auxin Response Interaktion AXR1-TIR1 Isolation TIR1 Isolation des TIR1 Gens Plasmid aus Agrobacterium tumefaciens, wird in Pflanzengenom inseriert und tumorartiges Wachstum aus Anwendung: T-DNA Abschnitt kann mit beliebiger DNA- Sequenz ausgetauscht werden, diese wird dann in pflanzliches Genom inseriert Herstellung einer Population T-DNA transformierter Pflanzen Griffiths, Introduction to Genetic Analysis, 10. Auflage, 2011
18 TIR1 Mutation Semidominanz Auxin Response Interaktion AXR1-TIR1 Isolation TIR1 Griffiths, Introduction to Genetic Analysis, 10. Auflage, 2011 Genetische Analyse: Single T-DNA Insert cosegregiert mit tir1-9 Mutante
19 TIR1 Mutation Semidominanz Auxin Response Interaktion AXR1-TIR1 Isolation TIR1 Plasmid Rescue Method 1. Plasmid in Genom inserieren 2. DNA isolieren und mit Restriktionsenzym verdauen 3. Fragment mit Ligase circularisieren Electroporation Methode zum Einbringen fremder DNA in eine Zelle. Durch Anlegen einen kurzen elektrischen Impulses wird die Membran durchlässig und die DNA kann in die Zelle diffundieren. 4. Neue Plasmide in E.coli übertragen (z.b. durch Electroporation) und auf Selektionsmedium wachsen lassen Quelle: ( )
20 Vorgehensweise DNA extrahieren SalI Restriktionsenzym Ligation mit T4 DNA ligase EcoRI Electroporation in JS4 E. coli Ausplattieren auf Selektionsmedium 4 colonies recovered (L1-L4) > 100 colonies recovered 5,5-kb Fragment von L3 = RFLP zwischen Wildtyp und tir1-9 Analyse Plasmid DNA (Ausschluss reiner T-DNA) L1-L4 R1-R14 Verwendung als Sonde in Southern Blot L3 und L4 gleiche restriction digest patterns
21 TIR1 Mutation Semidominanz Auxin Response Interaktion AXR1-TIR1 Isolation TIR1 Polymorphismus zwischen Wildtyp und tir1-9 T-DNA Insert liegt neben Gen Isolierung von cdna-klonen: Extrahieren von RNA; Reverse Transkriptase Screening mit 5,5-kb Fragment als Sonde cdna Library längste erhaltene cdna: 2,2 kb Sequenzierung: ORF (Open Reading Frame), kodiert für Protein mit 594 Aminosäuren Verifizierung: Vergleich mit zwei tir1 Allelen (tir1-1 und tir1-2) mittels RT-PCR (Reverser Transkriptase PCR) Außerdem: Sequenzanalyse von genomischem Klon Gen enthält 2 Introns, T-DNA Insert liegt in Intron 1
22 TIR1 Mutation Semidominanz Auxin Response Interaktion AXR1-TIR1 Isolation TIR1 Analyse TIR1 Die Aminosäuresequenz des kodierten Proteins TIR1 tir1-1: G147D tir1-2: G441D
23 TIR1 Mutation Semidominanz Auxin Response Interaktion AXR1-TIR1 Isolation TIR1 Analyse TIR1 Northern Blot Analyse In WT, tir1-2 und tir1-7, Transkript mit Länge ca. 2,2 kb In tir1-9 kein Transkript Kein Protein
24 TIR1 Mutation Semidominanz Auxin Response Interaktion AXR1-TIR1 Isolation TIR1 Analyse TIR1 Wiederherstellung des Wildtyps? TIR1 cdna wurde an CaMV 35S Promotor gekoppelt und in tir1-1 eingebracht In 4 von 5 Mutanten konnte der Wildtyp-Phänotyp wieder hergestellt werden! DNA stammt tatsächlich vom TIR1 Gen
25 TIR1 Mutation Semidominanz Auxin Response Interaktion AXR1-TIR1 Isolation TIR1 Analyse TIR1 TIR1 - Sequenzvergleich mit anderen Proteinen Analogien zu bekannten regulatorischen Proteinen aus Säugetieren und Hefe Gemeinsamkeit: F-box Binden an SKP1 SKP2, Cyclin F Cdc4, Grr1 UFO Mensch Hefe Arabidopsis bindet an SKP1-Orthologe ASK1 und ASK2
26 TIR1 Mutation Semidominanz Auxin Response Interaktion AXR1-TIR1 Isolation TIR1 Analyse TIR1 Sequenzvergleich mit anderen Proteinen TIR1 besitzt 16 leucinreiche repeats (LRR) Ähnlichkeit vielen weiteren Proteinen Allerdings große Unterschiede in Sequenz, Häufigkeit, Länge
27 TIR1 Mutation Semidominanz Auxin Response Interaktion AXR1-TIR1 Isolation TIR1 Analyse TIR1 Sequenzvergleich mit anderen Proteinen Homologien zwischen TIR1, C02F5.7, SKP2 und Grr1 C02F5.7, SKP2 und Grr1 binden an SKP1 SCF-Komplex (SKP1-Cdc53-F-box) als Ubiquitin-Proteinligase-Komplex vermutet Fungiert TIR1 im Ubiquitinpathway?
28 TIR1 Mutation Semidominanz Auxin Response Interaktion AXR1-TIR1 Isolation TIR1 Analyse TIR1 TIR1 - Sequenzvergleich mit anderen Genen Sequenzvergleiche liefern außerdem TIR1-ähnliche Gene in Arabidopsis LEUCINE-RICH REPEAT F-BOX (LRF) LRF1 und LRF2 als ESTs identifiziert (Expressed Sequence Tags) cdna-analyse ergab keine vollständige kodierende Sequenz bekannt: Transkripte von LRF1, LRF2 und TIR1 gleich groß Schätzung: 50 Nukleotide fehlen am 5 -Ende beider cdnas Übereinstimmung mit TIR1: LRF1 69 % LRF2 60 % LRF3 34 % ebenfalls große Ähnlichkeiten mit EST in Reis
29 Diskussion tir1 Defekte in auxinvermittelten Prozessen Hypokotylverlängerung Auxinhemmung bei Wurzelwachstum CPD-vermittelte Zellproliferation in der Wurzelspitze Lateralwurzelbildung Zellelongation (Hypokotylverlängerung) und Zellteilung (Zellproliferation in Wurzelspitze) betroffen Allgemeine Rolle in Auxinantwort TIR1 scheint in tir1-9 ganz zu fehlen TIR1 nicht essentiell für Auxinantwort Semidominanz der Mutation LRF redundant mit TIR1 Arabidopsis sensitiv für TIR1 Gendosis
30 F-Box-Proteine binden an SKP1 und bilden einen Ubiquitin-Protein-Ligase-Komplex (SCF) in Arabidopsis zwei SKP1- und ein CDC53-Homologe gefunden TIR1 könnte als Teil des Ubiquitin-Protein-Ligase-Komplexes in Ubiquitinpathway involviert sein E3 im Ubiquitinpathway zur Erinnerung: AXR1 könnte mit anderem Protein interagieren, das aktiven Cysteinrest enthält aktiviert als E1-Dimer Ubiquitin oder ubiquitinähnliches Protein AXR1 und TIR1 könnten als Teile der E1- bzw. E3-Komplexe bei der Ubiquitinierung von Proteinen fungieren
31 Modell AXR1 SCF-Komplex Hypothese TIR1 Auxin Response abhängig von ubiquitinvermitteltem Abbau von regulatorischen Proteinen Mögliches Zielprotein: Produkt von SAR1
32 Weitere Fragen Was ist die genaue Funktion der Ubiquitinierung? Welches ist das Zielprotein? Welche sind die weiteren Komponenten des Signalweges?
Hypothetische Modelle
 Hypothetische Modelle Heutiges Paper Vorgehensweise: Screening nach neuen Mutanten mit neuen Phänotyp Neuer Phänotyp: CPD, NPA- Resistenz (CPD, NPA: Wachstumshemmung durch Inhibierung des Auxin- Transport
Hypothetische Modelle Heutiges Paper Vorgehensweise: Screening nach neuen Mutanten mit neuen Phänotyp Neuer Phänotyp: CPD, NPA- Resistenz (CPD, NPA: Wachstumshemmung durch Inhibierung des Auxin- Transport
Präsentiert von Christina Staudigl
 Präsentiert von Christina Staudigl Was bisher geschah 2 Was bisher geschah Neues aus der Signaltransduktion? - nichts wirklich grundlegendes Aber: mehr ARFs gefunden (10x) mit leichten Unterschieden in
Präsentiert von Christina Staudigl Was bisher geschah 2 Was bisher geschah Neues aus der Signaltransduktion? - nichts wirklich grundlegendes Aber: mehr ARFs gefunden (10x) mit leichten Unterschieden in
The TIR1 protein of Arabidopsis functions in auxin response and is related to human SKP2 and
 The TIR1 protein of Arabidopsis functions in auxin response and is related to human SKP2 and yeast Grr1p Publikation von Max Ruegger, Elizabeth Dewey, William M. Gray, Lawrence Hobbie, Jocelyn Turner und
The TIR1 protein of Arabidopsis functions in auxin response and is related to human SKP2 and yeast Grr1p Publikation von Max Ruegger, Elizabeth Dewey, William M. Gray, Lawrence Hobbie, Jocelyn Turner und
Das Paper von heute. Samuel Grimm & Jan Kemna
 Das Paper von heute Samuel Grimm & Jan Kemna Bisheriges Modell Was bereits bekannt war - TIR1 ist an Auxinantwort (Zellteilung, Elongation, Differenzierung) beteiligt, im selben Signalweg wie AXR1 - TIR1
Das Paper von heute Samuel Grimm & Jan Kemna Bisheriges Modell Was bereits bekannt war - TIR1 ist an Auxinantwort (Zellteilung, Elongation, Differenzierung) beteiligt, im selben Signalweg wie AXR1 - TIR1
Hypothetische Modelle
 Hypothetische Modelle Hypothetische Modelle Das Paper Identification of an SCF ubiquitin ligase complex required for auxin response in Arabidopsis thaliana William M. Gray,1,4 J. Carlos del Pozo,1,4 Loni
Hypothetische Modelle Hypothetische Modelle Das Paper Identification of an SCF ubiquitin ligase complex required for auxin response in Arabidopsis thaliana William M. Gray,1,4 J. Carlos del Pozo,1,4 Loni
Stand von letzter Woche
 RUB ECR1 AXR1 Stand von letzter Woche E2 U? E1-like AXR1 Repressor ARF1 Proteasom AuxRE Repressor wird sehr schnell abgebaut notwendig für Auxinantwort evtl. Substrat für SCF Identifikation des SCF-Ubiquitin
RUB ECR1 AXR1 Stand von letzter Woche E2 U? E1-like AXR1 Repressor ARF1 Proteasom AuxRE Repressor wird sehr schnell abgebaut notwendig für Auxinantwort evtl. Substrat für SCF Identifikation des SCF-Ubiquitin
Seminar Molekulare Mechanismen der Signaltransduktion
 Seminar Molekulare Mechanismen der Signaltransduktion Gliederung (27.04.2010): Allgemeine Einleitung (Auxin, Nomenklatur...) Vorstellung der ersten paper Termine verteilen 1. Estelle and Somerville, (1987)
Seminar Molekulare Mechanismen der Signaltransduktion Gliederung (27.04.2010): Allgemeine Einleitung (Auxin, Nomenklatur...) Vorstellung der ersten paper Termine verteilen 1. Estelle and Somerville, (1987)
Organisation von Pflanzen wird während der Embryogenese ausgebildet
 Organisation von Pflanzen wird während der Embryogenese ausgebildet Musterung: Apikal (Shootmeristem, Kotelydonen) Mitte (Hypokotyl, Wurzelmeristem) Basal (Wurzelmeristem) Ablauf der Embryogenese in Arabidopsis
Organisation von Pflanzen wird während der Embryogenese ausgebildet Musterung: Apikal (Shootmeristem, Kotelydonen) Mitte (Hypokotyl, Wurzelmeristem) Basal (Wurzelmeristem) Ablauf der Embryogenese in Arabidopsis
Hypothetisches Modell
 Hypothetisches Modell Das Heutige Paper Inhalt: SCF bindet Auxin direkt TIR1 ist ein Auxin Rezeptor Auxin bindet direkt an TIR1, es sind keine zusätzlichen Komponenten nötig Methode Normales Pull down
Hypothetisches Modell Das Heutige Paper Inhalt: SCF bindet Auxin direkt TIR1 ist ein Auxin Rezeptor Auxin bindet direkt an TIR1, es sind keine zusätzlichen Komponenten nötig Methode Normales Pull down
Molekulare Mechanismen der Signaltransduktion. 06 - Kartierung des AXR1 Gens + early auxin-induced genes Folien: http://tinyurl.
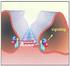 Molekulare Mechanismen der Signaltransduktion 06 - Kartierung des AXR1 Gens + early auxin-induced genes Folien: http://tinyurl.com/modul-mms bisheriges Modell auxin auxin AXR1 auxin response AXR1 potentieller
Molekulare Mechanismen der Signaltransduktion 06 - Kartierung des AXR1 Gens + early auxin-induced genes Folien: http://tinyurl.com/modul-mms bisheriges Modell auxin auxin AXR1 auxin response AXR1 potentieller
The Arabidopsis F-box protein TIR1 is an auxin receptor. Von Stefan Kepinski & Ottoline Leyser
 The Arabidopsis F-box protein TIR1 is an auxin receptor Von Stefan Kepinski & Ottoline Leyser Bekanntes Modell Was war bekannt? In der Zwischenzeit gefunden: - ABP1 kann große Mengen Auxin binden und ist
The Arabidopsis F-box protein TIR1 is an auxin receptor Von Stefan Kepinski & Ottoline Leyser Bekanntes Modell Was war bekannt? In der Zwischenzeit gefunden: - ABP1 kann große Mengen Auxin binden und ist
VORANGEGANGENE MODELLE
 VORANGEGANGENE MODELLE UNSER THEMA HEUTE Ziel dieses Papers: - Nähere Charakterisierung der AuxREs - Analyse eines zu den AuxREs gehörenden Transkriptionsfaktors WAS BEREITS BEKANNT WAR: - Auxin moduliert
VORANGEGANGENE MODELLE UNSER THEMA HEUTE Ziel dieses Papers: - Nähere Charakterisierung der AuxREs - Analyse eines zu den AuxREs gehörenden Transkriptionsfaktors WAS BEREITS BEKANNT WAR: - Auxin moduliert
Vorwärts /Rückwärts Mutationen. Somatische Zellen oder Keimzellen. Loss of function/gain of function. Mutagenese
 9. Mutationen Konzepte: Vorwärts /Rückwärts Mutationen Somatische Zellen oder Keimzellen Loss of function/gain of function Mutagenese 1. Loss of function Mutationen treten häufiger auf als gain of function
9. Mutationen Konzepte: Vorwärts /Rückwärts Mutationen Somatische Zellen oder Keimzellen Loss of function/gain of function Mutagenese 1. Loss of function Mutationen treten häufiger auf als gain of function
Molekulare Mechanismen der Signaltransduktion
 Molekulare Mechanismen der Signaltransduktion 05 - Auxin, EMS Mutagenese, Isolierung und Charakterisierung der axr1 Mutante Folien: http://tinyurl.com/modul-mms http://daisydukesgardens.files.wordpress.com/2013/01/phototropism.png
Molekulare Mechanismen der Signaltransduktion 05 - Auxin, EMS Mutagenese, Isolierung und Charakterisierung der axr1 Mutante Folien: http://tinyurl.com/modul-mms http://daisydukesgardens.files.wordpress.com/2013/01/phototropism.png
Molekulare Mechanismen der Signaltransduktion
 Molekulare Mechanismen der Signaltransduktion 07 - Identifizierung von ARF1 + Hinweise für Vorträge Folien: http://tinyurl.com/modul-mms http://www.pnas.org/content/111/14/5427/f1.large.jpg neues Modell
Molekulare Mechanismen der Signaltransduktion 07 - Identifizierung von ARF1 + Hinweise für Vorträge Folien: http://tinyurl.com/modul-mms http://www.pnas.org/content/111/14/5427/f1.large.jpg neues Modell
Genetik Praktikumsklausur SS2005
 Genetik Praktikumsklausur SS2005 1. Aufgabe: Der Genotyp AbaB wird geselbstet, dabei werden 256 Nachkommen gebildet. Davon erhalten 16 Pflanzen den Genotyp ABAB a) gekoppelt b) nicht gekoppelt c) teilweise
Genetik Praktikumsklausur SS2005 1. Aufgabe: Der Genotyp AbaB wird geselbstet, dabei werden 256 Nachkommen gebildet. Davon erhalten 16 Pflanzen den Genotyp ABAB a) gekoppelt b) nicht gekoppelt c) teilweise
Anhang Anhang 8.1 Konstruktion transgener SQD1 -Pflanzen
 Anhang 92 8 Anhang 8.1 Konstruktion transgener SQD1-Pflanzen Mutagenese und ein dadurch entstehender Phänotyp eines Organismus kann Aufschluß über die Funktion eines betroffenen Gens geben. Die Erzeugung
Anhang 92 8 Anhang 8.1 Konstruktion transgener SQD1-Pflanzen Mutagenese und ein dadurch entstehender Phänotyp eines Organismus kann Aufschluß über die Funktion eines betroffenen Gens geben. Die Erzeugung
Praktikum Biologen Gruppe B5
 Praktikum Biologen Gruppe B5 Versuch Betreuer Experiment Raum Tag Zeit BR1 & Langhammer Escherichia coli: 106 17.3. 13-17 BR2 Komplementationsanalyse von Lac-Mutanten Escherichia coli: Hfr-Kreuzung (P2)
Praktikum Biologen Gruppe B5 Versuch Betreuer Experiment Raum Tag Zeit BR1 & Langhammer Escherichia coli: 106 17.3. 13-17 BR2 Komplementationsanalyse von Lac-Mutanten Escherichia coli: Hfr-Kreuzung (P2)
Übung 11 Genregulation bei Prokaryoten
 Übung 11 Genregulation bei Prokaryoten Konzepte: Differentielle Genexpression Positive Genregulation Negative Genregulation cis-/trans-regulation 1. Auf welchen Ebenen kann Genregulation stattfinden? Definition
Übung 11 Genregulation bei Prokaryoten Konzepte: Differentielle Genexpression Positive Genregulation Negative Genregulation cis-/trans-regulation 1. Auf welchen Ebenen kann Genregulation stattfinden? Definition
Entwicklungs /gewebespezifische Genexpression. Coexpression funktional überlappender Gene
 Übung 11 Genregulation bei Prokaryoten Konzepte: Entwicklungs /gewebespezifische Genexpression Coexpression funktional überlappender Gene Positive Genregulation Negative Genregulation cis /trans Regulation
Übung 11 Genregulation bei Prokaryoten Konzepte: Entwicklungs /gewebespezifische Genexpression Coexpression funktional überlappender Gene Positive Genregulation Negative Genregulation cis /trans Regulation
Untersuchungen zur Funktion von Stärke-Synthasen in der Kartoffel (Solanum tuberosum L.)
 Untersuchungen zur Funktion von Stärke-Synthasen in der Kartoffel (Solanum tuberosum L.) Inaugural-Dissertation Erlangung der Doktorwürde im Fachbereich Biologie der Freien Univeisität Berlin vorgelegt
Untersuchungen zur Funktion von Stärke-Synthasen in der Kartoffel (Solanum tuberosum L.) Inaugural-Dissertation Erlangung der Doktorwürde im Fachbereich Biologie der Freien Univeisität Berlin vorgelegt
Jens Tilsner (Autor) Aminosäuretransport in Raps unter besonderer Berücksichtigung des Entwicklungsstadiums der Pflanze und der Stickstoffdüngung
 Jens Tilsner (Autor) Aminosäuretransport in Raps unter besonderer Berücksichtigung des Entwicklungsstadiums der Pflanze und der Stickstoffdüngung https://cuvillier.de/de/shop/publications/3133 Copyright:
Jens Tilsner (Autor) Aminosäuretransport in Raps unter besonderer Berücksichtigung des Entwicklungsstadiums der Pflanze und der Stickstoffdüngung https://cuvillier.de/de/shop/publications/3133 Copyright:
Transgene Organismen
 Transgene Organismen Themenübersicht 1) Einführung 2) Komplementäre DNA (cdna) 3) Vektoren 4) Einschleusung von Genen in Eukaryontenzellen 5) Ausmaß der Genexpression 6) Genausschaltung (Gen-Knockout)
Transgene Organismen Themenübersicht 1) Einführung 2) Komplementäre DNA (cdna) 3) Vektoren 4) Einschleusung von Genen in Eukaryontenzellen 5) Ausmaß der Genexpression 6) Genausschaltung (Gen-Knockout)
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 7 (11.07-15.07.) Methoden und Techniken II 1. Sie bekommen
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 7 (11.07-15.07.) Methoden und Techniken II 1. Sie bekommen
Identifikation von Krankheitsgenen
 Identifikation von Krankheitsgenen bei monogenen Erkrankungen Definition eines Kandidatengens Mutationsanalyse von genomischer- oder cdna bei miteinander nicht verwandten Patienten Identifikation der,
Identifikation von Krankheitsgenen bei monogenen Erkrankungen Definition eines Kandidatengens Mutationsanalyse von genomischer- oder cdna bei miteinander nicht verwandten Patienten Identifikation der,
Stammzüchtung. Selektion von natürlichen Varianten. Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese
 Stammzüchtung Selektion von natürlichen Varianten Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese Kreuzungen genetische Rekombination Sexuelle Kreuzungen Induzierte Zellfusion
Stammzüchtung Selektion von natürlichen Varianten Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese Kreuzungen genetische Rekombination Sexuelle Kreuzungen Induzierte Zellfusion
Antibiotika sind oft Inhibitoren der Genexpression
 Antibiotika sind oft Inhibitoren der Genexpression Inhibitoren der Transkription: Rifampicin, Actinomycin α-amanitin Inhibitoren der Translation: Puromycin, Streptomycin, Tetracycline, Chloramphenicol
Antibiotika sind oft Inhibitoren der Genexpression Inhibitoren der Transkription: Rifampicin, Actinomycin α-amanitin Inhibitoren der Translation: Puromycin, Streptomycin, Tetracycline, Chloramphenicol
Cornel Mülhardt. Genomics. 6. Auflaqe. Spektrum k - / l AKADEMISCHER VERLAG
 I Cornel Mülhardt Genomics 6. Auflaqe Spektrum k - / l AKADEMISCHER VERLAG Inhalt 1 Was ist denn "Molekularbiologie", bitteschön? 1 1.1 Das Substrat der Molekularbiologie, oder: Molli-World für Anfänger...
I Cornel Mülhardt Genomics 6. Auflaqe Spektrum k - / l AKADEMISCHER VERLAG Inhalt 1 Was ist denn "Molekularbiologie", bitteschön? 1 1.1 Das Substrat der Molekularbiologie, oder: Molli-World für Anfänger...
Molekularbiologie/ Genomics
 Cornel Mülhardt Molekularbiologie/ Genomics 5. Auflage ELSEVIER SPEKTRUM AKADEMISCHER VERLAG Spektrum k-zlakademischer VERLAG Inhalt 1 Was ist denn "Molekularbiologie", bitteschön? 1 1.1 Das Substrat der
Cornel Mülhardt Molekularbiologie/ Genomics 5. Auflage ELSEVIER SPEKTRUM AKADEMISCHER VERLAG Spektrum k-zlakademischer VERLAG Inhalt 1 Was ist denn "Molekularbiologie", bitteschön? 1 1.1 Das Substrat der
Klonierung von S2P Rolle der M19-Zellen. POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel
 Klonierung von S2P Rolle der M19-Zellen POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel Inhalt 1. Was ist eine humane genomische DNA-Bank? 2. Unterschied zwischen cdna-bank und genomischer DNA-Bank?
Klonierung von S2P Rolle der M19-Zellen POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel Inhalt 1. Was ist eine humane genomische DNA-Bank? 2. Unterschied zwischen cdna-bank und genomischer DNA-Bank?
Bioinformatik I: Grundlagen der Gentechnik
 Bioinformatik I: Grundlagen der Gentechnik Dr. Maik Böhmer Institut für Biologie und Biotechnologie der Pflanzen Schlossplatz 7 Schwerpunkte: Vorlesung 1: Einführung & Enzyme der Gentechnik Vorlesung 2:
Bioinformatik I: Grundlagen der Gentechnik Dr. Maik Böhmer Institut für Biologie und Biotechnologie der Pflanzen Schlossplatz 7 Schwerpunkte: Vorlesung 1: Einführung & Enzyme der Gentechnik Vorlesung 2:
Sophia Buhs. Dissertation. Diplom-Biochemikerin
 Beeinflussung Phosphotyrosin-abhängiger Signalwege in humanen unter Einsatz von SH2-Domänen und Phosphatasen in Kombination mit dem TAT-Transduktionssystem Dissertation Zur Erlangung der Würde des Doktors
Beeinflussung Phosphotyrosin-abhängiger Signalwege in humanen unter Einsatz von SH2-Domänen und Phosphatasen in Kombination mit dem TAT-Transduktionssystem Dissertation Zur Erlangung der Würde des Doktors
Zellstreckung/Phototropismus
 Zellstreckung/Phototropismus Phototropismus Zeitrafferaufnahmen von Haferkoleoptilen, die von links mit Blaulicht bestrahlt wurden. Effektiv: Blaulicht Krümmung erfolgt durch Zellstreckung auf der dem
Zellstreckung/Phototropismus Phototropismus Zeitrafferaufnahmen von Haferkoleoptilen, die von links mit Blaulicht bestrahlt wurden. Effektiv: Blaulicht Krümmung erfolgt durch Zellstreckung auf der dem
9. Mutationen. Konzepte: Vorwärts-/Rückwärts-Mutationen. Somatische Zellen oder Keimzellen. Loss-of-function/gain-of-function.
 9. Mutationen Konzepte: Vorwärts-/Rückwärts-Mutationen Somatische Zellen oder Keimzellen Loss-of-function/gain-of-function Mutagenese 1. Loss-of-function -Mutationen treten häufiger auf als gain-of-function
9. Mutationen Konzepte: Vorwärts-/Rückwärts-Mutationen Somatische Zellen oder Keimzellen Loss-of-function/gain-of-function Mutagenese 1. Loss-of-function -Mutationen treten häufiger auf als gain-of-function
Wechselwirkungen zwischen Genen. Chapter 6 Opener
 Wechselwirkungen zwischen Genen Chapter 6 Opener Kurze Wiederholung: Mutationen Haplosuffizienter Gene sind oft rezessiv! DNA RNA Protein Funktional Figure Funktional 6-2 Defekt Funktional Defekt Defekt
Wechselwirkungen zwischen Genen Chapter 6 Opener Kurze Wiederholung: Mutationen Haplosuffizienter Gene sind oft rezessiv! DNA RNA Protein Funktional Figure Funktional 6-2 Defekt Funktional Defekt Defekt
Restriktion und Gentechnik
 Restriktion und Gentechnik Einteilung 1.) Restriktion - Restriktionsenzyme - Southern Blotting 2.)Gentechnik - sticky ends - blunt ends Restriktion Grundwerkzeuge der Gentechnik - Restriktionsenzymanalyse
Restriktion und Gentechnik Einteilung 1.) Restriktion - Restriktionsenzyme - Southern Blotting 2.)Gentechnik - sticky ends - blunt ends Restriktion Grundwerkzeuge der Gentechnik - Restriktionsenzymanalyse
Übung 11 Genregulation bei Prokaryoten
 Übung 11 Genregulation bei Prokaryoten Konzepte: Differentielle Genexpression Positive Genregulation Negative Genregulation cis-/trans-regulation 1. Auf welchen Ebenen kann Genregulation stattfinden? Definition
Übung 11 Genregulation bei Prokaryoten Konzepte: Differentielle Genexpression Positive Genregulation Negative Genregulation cis-/trans-regulation 1. Auf welchen Ebenen kann Genregulation stattfinden? Definition
2. Seminar:
 2. Seminar: 04.05.2010 1. Ballaset al. (1993): Identification of the Auxin-responsive Element, AuxRE, in the Primary indoleacetic Acid-inducible Gene, PS- IAA4/5, of Pea (Pisumsativum). J Mol Biol 233:
2. Seminar: 04.05.2010 1. Ballaset al. (1993): Identification of the Auxin-responsive Element, AuxRE, in the Primary indoleacetic Acid-inducible Gene, PS- IAA4/5, of Pea (Pisumsativum). J Mol Biol 233:
Beschreiben Sie in Stichworten zwei der drei Suppressormutationen, die man in Hefe charakterisiert hat. Starzinski-Powitz, 6 Fragen, 53 Punkte Name
 Starzinski-Powitz, 6 Fragen, 53 Punkte Name Frage 1 8 Punkte Nennen Sie 2 Möglichkeiten, wie der Verlust von Heterozygotie bei Tumorsuppressorgenen (Z.B. dem Retinoblastomgen) zum klompletten Funktionsverlust
Starzinski-Powitz, 6 Fragen, 53 Punkte Name Frage 1 8 Punkte Nennen Sie 2 Möglichkeiten, wie der Verlust von Heterozygotie bei Tumorsuppressorgenen (Z.B. dem Retinoblastomgen) zum klompletten Funktionsverlust
Inhalt. 3 Das Werkzeug... 47 3.1 Restriktionsenzyme... 47 3.2 Gele... 58 3.2.1 Agarosegele... 58
 Inhalt 1 Was ist denn Molekularbiologie, bitteschön?...................... 1 1.1 Das Substrat der Molekularbiologie, oder: Molli-World für Anfänger.... 2 1.2 Was brauche ich zum Arbeiten?..................................
Inhalt 1 Was ist denn Molekularbiologie, bitteschön?...................... 1 1.1 Das Substrat der Molekularbiologie, oder: Molli-World für Anfänger.... 2 1.2 Was brauche ich zum Arbeiten?..................................
Hochdurchsatz Generierung und Analyse von Arabidopsis thaliana-proteinen
 MAX-PLANCK-INSTITUT FÜR MOLEKULARE GENETIK Hochdurchsatz Generierung und Analyse von Arabidopsis thaliana-proteinen Dissertation zur Erlangung der Doktorwürde des Fachbereichs Biologie, Chemie, Pharmazie
MAX-PLANCK-INSTITUT FÜR MOLEKULARE GENETIK Hochdurchsatz Generierung und Analyse von Arabidopsis thaliana-proteinen Dissertation zur Erlangung der Doktorwürde des Fachbereichs Biologie, Chemie, Pharmazie
Praktikum der Molekulargenetik
 Ulrich Kück (Hrsg.) Praktikum der Molekulargenetik unter der Mitarbeit von A. Bunse, H. Holländer-Czytko, S. Jeske, C. Klämbt, R. Klapper, I. Kubigsteltig, F. Meinhardt, J. Nickelsen, M. Nowrousian, S.
Ulrich Kück (Hrsg.) Praktikum der Molekulargenetik unter der Mitarbeit von A. Bunse, H. Holländer-Czytko, S. Jeske, C. Klämbt, R. Klapper, I. Kubigsteltig, F. Meinhardt, J. Nickelsen, M. Nowrousian, S.
Gentechnische Methoden
 Desmond S. T. Nicholl Gentechnische Methoden 2. Auflage Aus dem Englischen übersetzt von Renate FitzRoy und Kurt Beginnen Spektrum Akademischer Verlag Heidelberg Berlin Inhalt Vorwort XI 1. 1.1 1.2 1.3
Desmond S. T. Nicholl Gentechnische Methoden 2. Auflage Aus dem Englischen übersetzt von Renate FitzRoy und Kurt Beginnen Spektrum Akademischer Verlag Heidelberg Berlin Inhalt Vorwort XI 1. 1.1 1.2 1.3
Methoden der Gentechnik
 Methoden der Gentechnik *** DNA-Rekombination und Klonierung *** 1. Allgemeine Grundprinzipien 1.1. Wesen der Gentechnik 1.2. Allgemeine Ziele der Gentechnik 1.3. Molekulare Voraussetzungen 1.4. Wichtige
Methoden der Gentechnik *** DNA-Rekombination und Klonierung *** 1. Allgemeine Grundprinzipien 1.1. Wesen der Gentechnik 1.2. Allgemeine Ziele der Gentechnik 1.3. Molekulare Voraussetzungen 1.4. Wichtige
Stammzüchtung. Selektion von natürlichen Varianten. Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese
 Stammzüchtung Selektion von natürlichen Varianten Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese Kreuzungen genetische Rekombination Sexuelle Kreuzungen Induzierte Zellfusion
Stammzüchtung Selektion von natürlichen Varianten Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese Kreuzungen genetische Rekombination Sexuelle Kreuzungen Induzierte Zellfusion
Diskussion 62 6 DISKUSSION
 Diskussion 62 6 DISKUSSION Kartierungsergebnisse Sowohl die Analyse von Deletionssyndromen, wie dem WAGR-Syndrom, als auch Beobachtungen von Allelverlusten der Region 11p13 14.1 in verschiedenen Tumoren
Diskussion 62 6 DISKUSSION Kartierungsergebnisse Sowohl die Analyse von Deletionssyndromen, wie dem WAGR-Syndrom, als auch Beobachtungen von Allelverlusten der Region 11p13 14.1 in verschiedenen Tumoren
Inhalt 1 Modellorganismen
 Inhalt 1 Modellorganismen....................................... 1 1.1 Escherichia coli....................................... 1 1.1.1 Historisches...................................... 3 1.1.2 Lebenszyklus.....................................
Inhalt 1 Modellorganismen....................................... 1 1.1 Escherichia coli....................................... 1 1.1.1 Historisches...................................... 3 1.1.2 Lebenszyklus.....................................
Michelle Kammel David Speck
 Michelle Kammel David Speck 10.07.2013 Was ist bisher bekannt? Zentrum des Signalwegs ist der Ubiquitin Ligase SCF TIR1 Komplex Gray et al. (2001) Abbau der Aux/IAA aktiviert Transkriptionsfaktoren (ARFs)
Michelle Kammel David Speck 10.07.2013 Was ist bisher bekannt? Zentrum des Signalwegs ist der Ubiquitin Ligase SCF TIR1 Komplex Gray et al. (2001) Abbau der Aux/IAA aktiviert Transkriptionsfaktoren (ARFs)
Alternative Methoden der RNA-Analyse
 Alternative Methoden der RNA-Analyse In diesem Versuch wurde die Northern Blot Hybridisierung zur Analyse isolierter mrna eingesetzt. Mit dieser Technik können Größe und Menge einer spezifischen RNA bestimmt
Alternative Methoden der RNA-Analyse In diesem Versuch wurde die Northern Blot Hybridisierung zur Analyse isolierter mrna eingesetzt. Mit dieser Technik können Größe und Menge einer spezifischen RNA bestimmt
Aufbau eines Assays zur Optimierung einer Polymerase für die Generierung hochgradig fluoreszenz-markierter DNA
 Aufbau eines Assays zur Optimierung einer Polymerase für die Generierung hochgradig fluoreszenz-markierter DNA Von der Naturwissenschaftlichen Fakultät der Technischen Universität Carolo-Wilhelmina zu
Aufbau eines Assays zur Optimierung einer Polymerase für die Generierung hochgradig fluoreszenz-markierter DNA Von der Naturwissenschaftlichen Fakultät der Technischen Universität Carolo-Wilhelmina zu
F2 aus der Kreuzung mit der ersten Mutante: 602 normal, 198 keine Blatthaare
 Klausur Genetik Name: Matrikelnummer: Sie haben 90 Minuten Zeit zur Bearbeitung der 23 Fragen (z. T. mit Unterpunkten). Insgesamt sind 42 Punkte zu vergeben. Die Klausur gilt als bestanden, falls 21 Punkte
Klausur Genetik Name: Matrikelnummer: Sie haben 90 Minuten Zeit zur Bearbeitung der 23 Fragen (z. T. mit Unterpunkten). Insgesamt sind 42 Punkte zu vergeben. Die Klausur gilt als bestanden, falls 21 Punkte
Grundlagen der Klonierung. Analytische Methoden der Biologie SS09 7 Klonierung und Gentechnik. Modul
 Restriktion und Ligation: Restriktion und Ligation: Grundlagen der Klonierung Modul 2303-021 1 Restriktion und Ligation Verknüpfung von Fragmenten unterschiedlicher DNA Herkunft Restriktion und Ligation
Restriktion und Ligation: Restriktion und Ligation: Grundlagen der Klonierung Modul 2303-021 1 Restriktion und Ligation Verknüpfung von Fragmenten unterschiedlicher DNA Herkunft Restriktion und Ligation
AUFGABENSAMMLUNG. Restriktionsenzyme. Füllen Sie den Lückentext aus. Gentechnik Schroedel, Braunschweig
 Restriktionsenzyme Füllen Sie den Lückentext aus. PCR 1a Mit dem folgenden Quiz können Sie Ihr Wissen zum Thema PCR überprüfen. Klicken Sie jeweils die richtige Antwort an. PCR 1b Mit dem folgenden Quiz
Restriktionsenzyme Füllen Sie den Lückentext aus. PCR 1a Mit dem folgenden Quiz können Sie Ihr Wissen zum Thema PCR überprüfen. Klicken Sie jeweils die richtige Antwort an. PCR 1b Mit dem folgenden Quiz
Veränderung der Zahl der Chromosomensätze (Polyploidisierung)
 Mutationen - Genommutationen - Chromosomenmutationen - Genmutationen (Punktmutationen) - Erkennbarkeit und Auswirkungen von Punktmutationen - neutrale Mutationen - Missense -Mutationen - Nonsense -Mutationen
Mutationen - Genommutationen - Chromosomenmutationen - Genmutationen (Punktmutationen) - Erkennbarkeit und Auswirkungen von Punktmutationen - neutrale Mutationen - Missense -Mutationen - Nonsense -Mutationen
Herstellung und Charakterisierung von zellpermeablem Interferon-α des Waldmurmeltieres (Marmota monax)
 Aus der Abteilung Innere Medizin II der Medizinischen Universitätsklinik der Albert-Ludwigs-Universität Freiburg im Breisgau Herstellung und Charakterisierung von zellpermeablem Interferon-α des Waldmurmeltieres
Aus der Abteilung Innere Medizin II der Medizinischen Universitätsklinik der Albert-Ludwigs-Universität Freiburg im Breisgau Herstellung und Charakterisierung von zellpermeablem Interferon-α des Waldmurmeltieres
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 4 (20.06. 24.06.) Regulation der Transkription II, Translation
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 4 (20.06. 24.06.) Regulation der Transkription II, Translation
Komplementation. Allelische Interaktionen. Gen Interaktionen
 3. Gen Interaktionen Konzepte: Komplementation Allelische Interaktionen Gen Interaktionen 1. Beschreiben Sie einen Mutagenese Screen (Genetic Screen). Wozu wird er angewendet? Ziel: Identifizierung von
3. Gen Interaktionen Konzepte: Komplementation Allelische Interaktionen Gen Interaktionen 1. Beschreiben Sie einen Mutagenese Screen (Genetic Screen). Wozu wird er angewendet? Ziel: Identifizierung von
RUHR-UNIVERSITÄT BOCHUM
 RUHR-UNIVERSITÄT BOCHUM Fakultät für Chemie Titel der Lehreinheit (LE) Modulpraktika Biochemie im Schwerpunkt Molekulare Biologie und Biotechnologie der Pflanzen und Mikroorganismen Molekularbiologie von
RUHR-UNIVERSITÄT BOCHUM Fakultät für Chemie Titel der Lehreinheit (LE) Modulpraktika Biochemie im Schwerpunkt Molekulare Biologie und Biotechnologie der Pflanzen und Mikroorganismen Molekularbiologie von
Pharmazeutische Biologie WS2011/2012. Das neue Paradigma: Personalisierte Medizin
 3. Vorlesung Pharmazeutische Biologie WS2011/2012 Das neue Paradigma: Personalisierte Medizin Prof. Theo Dingermann Institut für Pharmazeutische Biologie Biozentrum Max-von Laue-Str. 9 60438 Frankfurt
3. Vorlesung Pharmazeutische Biologie WS2011/2012 Das neue Paradigma: Personalisierte Medizin Prof. Theo Dingermann Institut für Pharmazeutische Biologie Biozentrum Max-von Laue-Str. 9 60438 Frankfurt
General Concepts to Dissect Signaling Pathways
 General Concepts to Dissect Signaling Pathways Forward Genetics Molecular Biology Biochemistry Receptors Early Genes Growth & Development Gene Expression Binding Proteins ( Biochemistry) ( Reverse Genetics)
General Concepts to Dissect Signaling Pathways Forward Genetics Molecular Biology Biochemistry Receptors Early Genes Growth & Development Gene Expression Binding Proteins ( Biochemistry) ( Reverse Genetics)
3 Ergebnisse. 3.1 Die Speckling-Domäne von Wt1 umfaßt die Aminosäuren
 3 Ergebnisse 3.1 Die Speckling-Domäne von Wt1 umfaßt die Aminosäuren 76-120 Die Existenz verschiedener Isoformen von WT1 ist unter anderem auf die Verwendung einer für die Aminosäuren KTS kodierenden alternativen
3 Ergebnisse 3.1 Die Speckling-Domäne von Wt1 umfaßt die Aminosäuren 76-120 Die Existenz verschiedener Isoformen von WT1 ist unter anderem auf die Verwendung einer für die Aminosäuren KTS kodierenden alternativen
DNA-Replikation. Konrad Beyreuther. Stefan Kins
 DNA-Replikation Konrad Beyreuther Stefan Kins DNA-Replikation Originalgetreue Verdopplung des genetischen Materials als Voraussetzung für die kontinuierliche Weitergabe der in der DNA verschlüsselten Information
DNA-Replikation Konrad Beyreuther Stefan Kins DNA-Replikation Originalgetreue Verdopplung des genetischen Materials als Voraussetzung für die kontinuierliche Weitergabe der in der DNA verschlüsselten Information
DNA-Fingerprint. (Syn. DNA Profiling)
 DNA-Fingerprint (Syn. DNA Profiling) Dient dazu Individuen genetisch zu unterscheiden Dazu braucht man genetischen Polymorphismus (Bsp. Blutgruppen-Polymorphismus/Landsteiner). Als Polymorphismus ( Vielgestaltigkeit
DNA-Fingerprint (Syn. DNA Profiling) Dient dazu Individuen genetisch zu unterscheiden Dazu braucht man genetischen Polymorphismus (Bsp. Blutgruppen-Polymorphismus/Landsteiner). Als Polymorphismus ( Vielgestaltigkeit
GEIM- TECHIMOLOGISCHE ARBEITSMETHODEN
 GEIM- TECHIMOLOGISCHE ARBEITSMETHODEN Ein Handbuch experimenteller Techniken und Verfahren Herausgegeben von Rudolf Hagemann Bearbeitet von Frank Baldauf, Jörn Belter, Sabine Brantl, Baimund Eck, Karsten
GEIM- TECHIMOLOGISCHE ARBEITSMETHODEN Ein Handbuch experimenteller Techniken und Verfahren Herausgegeben von Rudolf Hagemann Bearbeitet von Frank Baldauf, Jörn Belter, Sabine Brantl, Baimund Eck, Karsten
Gentechnologie für Einsteiger
 T. A. Brown Gentechnologie für Einsteiger 3. Auflage Aus dem Englischen übersetzt von Sebastian Vogel Spektrum Akademischer Verlag Heidelberg Berlin Vorwort Vorwort zur dritten englischen Auflage Vorwort
T. A. Brown Gentechnologie für Einsteiger 3. Auflage Aus dem Englischen übersetzt von Sebastian Vogel Spektrum Akademischer Verlag Heidelberg Berlin Vorwort Vorwort zur dritten englischen Auflage Vorwort
Neue Enzyme für ein altes Organeil: Kryptische peroxisomale Lokalisationssignale in Pilzen. Dissertation
 Neue Enzyme für ein altes Organeil: Kryptische peroxisomale Lokalisationssignale in Pilzen Dissertation zur Erlangung des Doktorgrades der Naturwissenschaften (Dr. rer. nat.) Dem Fachbereich Biologie der
Neue Enzyme für ein altes Organeil: Kryptische peroxisomale Lokalisationssignale in Pilzen Dissertation zur Erlangung des Doktorgrades der Naturwissenschaften (Dr. rer. nat.) Dem Fachbereich Biologie der
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr
 Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
3. Gen-Interaktionen
 3. Gen-Interaktionen Rückblick: 1Gene(2 Allele ) Merkmal1 1Gene(2 Allele ) Merkmal2 1 Gen (2 Allele = dominant + rezessiv) 1 Merkmal mit 2 Phänotypklassen bisher: keine Gen-/Allel-Interaktionen berücksichtigt!
3. Gen-Interaktionen Rückblick: 1Gene(2 Allele ) Merkmal1 1Gene(2 Allele ) Merkmal2 1 Gen (2 Allele = dominant + rezessiv) 1 Merkmal mit 2 Phänotypklassen bisher: keine Gen-/Allel-Interaktionen berücksichtigt!
Grundlegende Experimente der Molekulargenetik
 Übung 12 Wiederholung/Zusatzübung Inhalte: Mendelscher Erbgang Grundlegende Experimente der Molekulargenetik Transposons Methoden 1. Sie haben drei runde, gelbe Erbsen (A, B und C). Aus jeder der drei
Übung 12 Wiederholung/Zusatzübung Inhalte: Mendelscher Erbgang Grundlegende Experimente der Molekulargenetik Transposons Methoden 1. Sie haben drei runde, gelbe Erbsen (A, B und C). Aus jeder der drei
3 Ergebnisse. 3.1 Mutationen im MYBPC3-Gen. 28 Ergebnisse
 28 Ergebnisse 3 Ergebnisse 3.1 Mutationen im MYBPC3-Gen Bei einem Patientenkollektiv von insgesamt 46 unverwandten Patienten mit dilatativer Kardiomyopathie (DCM) wurde eine systematische Mutationssuche
28 Ergebnisse 3 Ergebnisse 3.1 Mutationen im MYBPC3-Gen Bei einem Patientenkollektiv von insgesamt 46 unverwandten Patienten mit dilatativer Kardiomyopathie (DCM) wurde eine systematische Mutationssuche
7. Anhang. 7. Anhang. Abbildung 7.1: Aminosäuresequenz AtMYC2 im Wildtyp und in jin1. Unterschiede zwischen den Sequenzen sind rot unterlegt.
 7. Anhang 10 20 30 40 50 60 70 80 90 100 jin1 MTDYRLQPTMNLWTTDDNASMMEAFMSSSDISTLWPPASTTTTTATTETTPTPAMEIPAQAGFNQETLQQRLQALIEGTHEGWTYAIFWQPSYDFSGASV AtMYC2 MTDYRLQPTMNLWTTDDNASMMEAFMSSSDISTLWPPASTTTTTATTETTPTPAMEIPAQAGFNQETLQQRLQALIEGTHEGWTYAIFWQPSYDFSGASV
7. Anhang 10 20 30 40 50 60 70 80 90 100 jin1 MTDYRLQPTMNLWTTDDNASMMEAFMSSSDISTLWPPASTTTTTATTETTPTPAMEIPAQAGFNQETLQQRLQALIEGTHEGWTYAIFWQPSYDFSGASV AtMYC2 MTDYRLQPTMNLWTTDDNASMMEAFMSSSDISTLWPPASTTTTTATTETTPTPAMEIPAQAGFNQETLQQRLQALIEGTHEGWTYAIFWQPSYDFSGASV
Molekulare Klonierung Praktikum
 Molekulare Klonierung Praktikum 2013 Praktikumsaufgabe Ligation 1. Zusammensetzung des Ligationsreaktions-ansatzes : 1 l Vektor DNA 1 l Insert DNA 2 l 10X Ligase Puffer 15 l destillertes Wasser 1 l Ligase
Molekulare Klonierung Praktikum 2013 Praktikumsaufgabe Ligation 1. Zusammensetzung des Ligationsreaktions-ansatzes : 1 l Vektor DNA 1 l Insert DNA 2 l 10X Ligase Puffer 15 l destillertes Wasser 1 l Ligase
1. Skizzieren Sie schematisch ein Gen mit flankierender Region. Bezeichnen und beschriften Sie:
 1. Skizzieren Sie schematisch ein Gen mit flankierender Region. Bezeichnen und beschriften Sie: - 5 UTR (leader) - 3 UTR (trailer) - Terminator - Stopp-Kodon - Initiationskodon - Transkriptionsstartstelle
1. Skizzieren Sie schematisch ein Gen mit flankierender Region. Bezeichnen und beschriften Sie: - 5 UTR (leader) - 3 UTR (trailer) - Terminator - Stopp-Kodon - Initiationskodon - Transkriptionsstartstelle
Proteinbiosynthese: Transkripion:
 Proteinbiosynthese: - Basensequenz der DNA wird in die Basensequenz der RNA übersetzt (Transkription) - Übersetzen der mrna in die spezifische Aminosäuresequenz (Translation) - Bei Eukaryoten sind Transkription
Proteinbiosynthese: - Basensequenz der DNA wird in die Basensequenz der RNA übersetzt (Transkription) - Übersetzen der mrna in die spezifische Aminosäuresequenz (Translation) - Bei Eukaryoten sind Transkription
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Vorbemerkung für die Erlangung des Testats: Bearbeiten Sie die unten gestellten Aufgaben
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Vorbemerkung für die Erlangung des Testats: Bearbeiten Sie die unten gestellten Aufgaben
Vorlesungsthemen Mikrobiologie
 Vorlesungsthemen Mikrobiologie 1. Einführung in die Mikrobiologie B. Bukau 2. Zellaufbau von Prokaryoten B. Bukau 3. Bakterielles Wachstum und Differenzierung B. Bukau 4. Bakterielle Genetik und Evolution
Vorlesungsthemen Mikrobiologie 1. Einführung in die Mikrobiologie B. Bukau 2. Zellaufbau von Prokaryoten B. Bukau 3. Bakterielles Wachstum und Differenzierung B. Bukau 4. Bakterielle Genetik und Evolution
3. Ergebnisse Ergebnisse. 3.1 MDR1-Polymorphismen
 . Ergebnisse. Ergebnisse. MDR-Polymorphismen Im Rahmen der Studie erfolgte die Untersuchung von Polymorphismen mittels PCR und RFLP und deren Auswirkung auf die Pharmakokinetik des P-gp-Substrates Digoxin.
. Ergebnisse. Ergebnisse. MDR-Polymorphismen Im Rahmen der Studie erfolgte die Untersuchung von Polymorphismen mittels PCR und RFLP und deren Auswirkung auf die Pharmakokinetik des P-gp-Substrates Digoxin.
MOSC-Proteine aus Escherichia coli, Homo sapiens, Mus musculus und. Arabidopsis thaliana
 Untersuchung Molybdäncofaktor-haltiger MOSC-Proteine aus Escherichia coli, Homo sapiens, Mus musculus und Arabidopsis thaliana Von der Fakultät für Lebenswissenschaften der Technischen Universität Carolo-Wilhelmina
Untersuchung Molybdäncofaktor-haltiger MOSC-Proteine aus Escherichia coli, Homo sapiens, Mus musculus und Arabidopsis thaliana Von der Fakultät für Lebenswissenschaften der Technischen Universität Carolo-Wilhelmina
LEHRSTUHL ZELLBIOLOGIE
 LEHRSTUHL ZELLBIOLOGIE Signalwahrnehmung & weiterleitung: Regulation zellulärer Prozesse Protisten (Euglena gracilis) Grünalgen (Chlamydomonas reinhardtii) Moose (Physcomitrella patens) Höhere Pflanzen
LEHRSTUHL ZELLBIOLOGIE Signalwahrnehmung & weiterleitung: Regulation zellulärer Prozesse Protisten (Euglena gracilis) Grünalgen (Chlamydomonas reinhardtii) Moose (Physcomitrella patens) Höhere Pflanzen
1. Einleitung S. 1 1.1. Zelladhäsionsmoleküle S. 1 1.2. Die Immunglobulin-Superfamilie S. 2. 1.2.1. Das neurale Zelladhäsionsmolekül NCAM S.
 Inhaltsverzeichnis 1. Einleitung S. 1 1.1. Zelladhäsionsmoleküle S. 1 1.2. Die Immunglobulin-Superfamilie S. 2 1.2.1. Das neurale Zelladhäsionsmolekül NCAM S. 4 1.2.1.1. Molekulare Struktur von NCAM S.
Inhaltsverzeichnis 1. Einleitung S. 1 1.1. Zelladhäsionsmoleküle S. 1 1.2. Die Immunglobulin-Superfamilie S. 2 1.2.1. Das neurale Zelladhäsionsmolekül NCAM S. 4 1.2.1.1. Molekulare Struktur von NCAM S.
1. Welche Auswirkungen auf die Expression des lac-operons haben die folgenden Mutationen:
 Übung 10 1. Welche Auswirkungen auf die Expression des lac-operons haben die folgenden Mutationen: a. Eine Mutation, die zur Expression eines Repressors führt, der nicht mehr an den Operator binden kann.
Übung 10 1. Welche Auswirkungen auf die Expression des lac-operons haben die folgenden Mutationen: a. Eine Mutation, die zur Expression eines Repressors führt, der nicht mehr an den Operator binden kann.
Phage-Display. Übersicht. Allgemeine Einführung Phage M13 Vektoren Bibliotheken Selektionsablauf Anwendungsmöglichkeiten.
 Phage-Display Thomas Haarmann AG Dietrich Methodenseminar Biochemie II 20.01. und 10.02.2009 Übersicht Allgemeine Einführung Phage M13 Vektoren Bibliotheken Selektionsablauf Anwendungsmöglichkeiten Phage-Display
Phage-Display Thomas Haarmann AG Dietrich Methodenseminar Biochemie II 20.01. und 10.02.2009 Übersicht Allgemeine Einführung Phage M13 Vektoren Bibliotheken Selektionsablauf Anwendungsmöglichkeiten Phage-Display
https://cuvillier.de/de/shop/publications/1657
 Christian Landmann (Autor) Funktionelle Charakterisierung von Enzymen des Sekundärstoffwechsels in Lavendel (Lavandula angustifolia) und Erdbeere (Fragaria x ananassa) https://cuvillier.de/de/shop/publications/1657
Christian Landmann (Autor) Funktionelle Charakterisierung von Enzymen des Sekundärstoffwechsels in Lavendel (Lavandula angustifolia) und Erdbeere (Fragaria x ananassa) https://cuvillier.de/de/shop/publications/1657
β2-microglobulin deficient mice lack CD4-8+cytolytic T cells
 β2-microglobulin deficient mice lack CD4-8+cytolytic T cells Mäuse mit einem Knock-out bezüglich ß-Microglobulin sind nicht in der Lage CD4-8+ cytotoxische T-Zellen zu bilden Nature,Vol 344, 19. April
β2-microglobulin deficient mice lack CD4-8+cytolytic T cells Mäuse mit einem Knock-out bezüglich ß-Microglobulin sind nicht in der Lage CD4-8+ cytotoxische T-Zellen zu bilden Nature,Vol 344, 19. April
Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR)
 PCR Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR) von Kary B. Mullis entwickelt (1985) eigentlich im Mai 1983 bei einer nächtlichen Autofahrt erstes erfolgreiches Experiment am 16.12.1983
PCR Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR) von Kary B. Mullis entwickelt (1985) eigentlich im Mai 1983 bei einer nächtlichen Autofahrt erstes erfolgreiches Experiment am 16.12.1983
Vertiefendes Seminar zur Vorlesung Biochemie I
 Vertiefendes Seminar zur Vorlesung Biochemie I 30.01.2015 Klausurvorbereitung: Gerhild van Echten-Deckert Rekombinante DNA Fon. +49-228-732703 Homepage: http://www.limes.uni-bonn.de Klärung einiger Begriffe:
Vertiefendes Seminar zur Vorlesung Biochemie I 30.01.2015 Klausurvorbereitung: Gerhild van Echten-Deckert Rekombinante DNA Fon. +49-228-732703 Homepage: http://www.limes.uni-bonn.de Klärung einiger Begriffe:
Inhaltsverzeichnis... I. Ein Vorwort... VII. Synopse der Arbeit... IX. Synopsis of the thesis... XIII
 I INHALTSVERZEICHNIS Inhaltsverzeichnis... I Ein Vorwort... VII Synopse der Arbeit... IX Synopsis of the thesis... XIII A. Untersuchungen über die Stereoselektivität bakterieller, Pyruvat-abhängiger Aldolasen...
I INHALTSVERZEICHNIS Inhaltsverzeichnis... I Ein Vorwort... VII Synopse der Arbeit... IX Synopsis of the thesis... XIII A. Untersuchungen über die Stereoselektivität bakterieller, Pyruvat-abhängiger Aldolasen...
1. Nennt Informationen, die ein Wissenschaftler für die Durchführung des farbig markierten Schrittes benötigt. 2. Nennt zusätzliche Probleme die bei
 Wir erinnern uns 1. Nennt Informationen, die ein Wissenschaftler für die Durchführung des farbig markierten Schrittes benötigt. 2. Nennt zusätzliche Probleme die bei der Verwendung eines Gens aus einer
Wir erinnern uns 1. Nennt Informationen, die ein Wissenschaftler für die Durchführung des farbig markierten Schrittes benötigt. 2. Nennt zusätzliche Probleme die bei der Verwendung eines Gens aus einer
Prüfungsfragenkatalog für für Grundlagen der Gentechnik und Biotechnologie (Prof. Prof. Rudolf Bauer und Prof. Karin Ardjomand-Wölkart)
 Prüfungsfragenkatalog für für Grundlagen der Gentechnik und Biotechnologie (Prof. Prof. Rudolf Bauer und Prof. Karin Ardjomand-Wölkart) Stand: September 2014 Termin: 29.09.2014 1. Was ist Western Blot?
Prüfungsfragenkatalog für für Grundlagen der Gentechnik und Biotechnologie (Prof. Prof. Rudolf Bauer und Prof. Karin Ardjomand-Wölkart) Stand: September 2014 Termin: 29.09.2014 1. Was ist Western Blot?
Mechanismen der Pasteurella multocida Toxin vermittelten Modulation des Osteoimmunsystems
 Mechanismen der Pasteurella multocida Toxin vermittelten Modulation des Osteoimmunsystems Gutachter Prof. Dr. Alexander Dalpke Prof. Dr. Ralf Bartenschlager Inhaltsverzeichnis 1 Zusammenfassung 1 2 Einleitung
Mechanismen der Pasteurella multocida Toxin vermittelten Modulation des Osteoimmunsystems Gutachter Prof. Dr. Alexander Dalpke Prof. Dr. Ralf Bartenschlager Inhaltsverzeichnis 1 Zusammenfassung 1 2 Einleitung
3. Gen-Interaktionen. Konzepte: Komplementation. Allelische Interaktionen. Gen-Interaktionen
 3. Gen-Interaktionen Konzepte: Komplementation Allelische Interaktionen Gen-Interaktionen 1. Beschreiben Sie einen Mutagenese Screen (Genetic Screen). Wozu wird er angewendet? Ziel: Identifizierung von
3. Gen-Interaktionen Konzepte: Komplementation Allelische Interaktionen Gen-Interaktionen 1. Beschreiben Sie einen Mutagenese Screen (Genetic Screen). Wozu wird er angewendet? Ziel: Identifizierung von
2. Konstruktion und Charakterisierung einer stx 2 -Mutante im E. coli-stamm O157:H7 86-24
 IV. Ergebnisse 90 2. Konstruktion und Charakterisierung einer stx 2 -Mutante im E. coli-stamm O157:H7 86-24 Die Konstruktion einer isogenen Toxinmutante des Stx2-produzierenden EHEC- Stamm O157:H7 86-24
IV. Ergebnisse 90 2. Konstruktion und Charakterisierung einer stx 2 -Mutante im E. coli-stamm O157:H7 86-24 Die Konstruktion einer isogenen Toxinmutante des Stx2-produzierenden EHEC- Stamm O157:H7 86-24
Genetische Kontrolle der Entwicklung mehrzelliger Eukaryonten
 1. Was sind maternale Effektgene, wann entstehen aus diesen Genen Genprodukte und wo sind diese lokalisiert? Welche Aspekte der Entwicklung steuern maternale Effektgene? Übung 12 Entwicklungsgenetik Genetische
1. Was sind maternale Effektgene, wann entstehen aus diesen Genen Genprodukte und wo sind diese lokalisiert? Welche Aspekte der Entwicklung steuern maternale Effektgene? Übung 12 Entwicklungsgenetik Genetische
MODULE für den SCHULKOFFER GENTECHNIK
 MODULE für den SCHULKOFFER GENTECHNIK Modul 1 - DNA-Bastel-Set Zusammenbau eines Papiermodells in Form einer Doppelhelix sehr einfach, Unterstufe, ohne Koffer möglich Modul 2 - DNA-Isolierung aus Gemüse
MODULE für den SCHULKOFFER GENTECHNIK Modul 1 - DNA-Bastel-Set Zusammenbau eines Papiermodells in Form einer Doppelhelix sehr einfach, Unterstufe, ohne Koffer möglich Modul 2 - DNA-Isolierung aus Gemüse
DNA Replikation ist semikonservativ. Abb. aus Stryer (5th Ed.)
 DNA Replikation ist semikonservativ Entwindung der DNA-Doppelhelix durch eine Helikase Replikationsgabel Eltern-DNA Beide DNA-Stränge werden in 5 3 Richtung synthetisiert DNA-Polymerasen katalysieren die
DNA Replikation ist semikonservativ Entwindung der DNA-Doppelhelix durch eine Helikase Replikationsgabel Eltern-DNA Beide DNA-Stränge werden in 5 3 Richtung synthetisiert DNA-Polymerasen katalysieren die
Vorlesung LV-Nr Molekularbiologie für Agrarwissenschaften. J. Glößl, SS 2007
 Vorlesung LV-Nr. 954.104 Molekularbiologie für Agrarwissenschaften J. Glößl, SS 2007 Thematik: Molekularbiologische Methoden Teil 2 Die ppt Folien wurden freundlicherweise von Prof. Florian Rüker aus der
Vorlesung LV-Nr. 954.104 Molekularbiologie für Agrarwissenschaften J. Glößl, SS 2007 Thematik: Molekularbiologische Methoden Teil 2 Die ppt Folien wurden freundlicherweise von Prof. Florian Rüker aus der
Vererbung. Die durch Fortpflanzung entstandene Nachkommenschaft gleicht den Elternorganismen weitgehend
 Vererbung Die durch Fortpflanzung entstandene Nachkommenschaft gleicht den Elternorganismen weitgehend Klassische Genetik Äußeres Erscheinungsbild: Phänotypus setzt sich aus einer Reihe von Merkmalen (Phänen))
Vererbung Die durch Fortpflanzung entstandene Nachkommenschaft gleicht den Elternorganismen weitgehend Klassische Genetik Äußeres Erscheinungsbild: Phänotypus setzt sich aus einer Reihe von Merkmalen (Phänen))
