Gebrauchsanleitung. Der schnelle Erregernachweis bei Verdacht auf Dermatomykosen. Für In-vitro-diagnostische Untersuchungen
|
|
|
- Sara Lichtenberg
- vor 6 Jahren
- Abrufe
Transkript
1 Mentype MycoDerm QS Gebrauchsanleitung Der schnelle Erregernachweis bei Verdacht auf Dermatomykosen Für In-vitro-diagnostische Untersuchungen Biotype Diagnostic GmbH Moritzburger Weg 67 D Dresden Germany Made in Germany
2 2 Die Biotype Diagnostic GmbH entwickelt molekularbiologische In-vitro- Diagnostik (IVD) für Hämatologie/Onkologie, Dermatologie und Urologie. Das Unternehmen greift dabei auf langjährige Erfahrung in der Entwicklung und Produktion von Testsystemen in der DNA-Analytik zurück. In Zusammenarbeit mit wissenschaftlichen Experten wird der Anspruch der ganzheitlichen Diagnostik in innovative Produktideen und qualitativ hochwertige, kundenorientierte Anwendungen umgesetzt. Unsere Produktgruppen Mentype und Sampletype stehen für höchste Qualität in der klinischen Diagnostik. Für weitere Informationen und Fragen bzgl. Mentype MycoDerm QS stehen wir Ihnen jederzeit gerne zur Verfügung:
3 3 Warenzeichen und Patente Mentype und i-sep sind eingetragene Warenzeichen der Biotype Diagnostic GmbH. Ficoll ist ein eingetragenes Warenzeichen der GE Healthcare Bio-170 Sciences AB. GelRed TM ist ein eingetragenes Warenzeichen der Biotium Inc. GeneAmp ist ein eingetragenes Warenzeichen von Roche Molecular Systems. Mastercycler ist ein eingetragenes Warenzeichen der Eppendorf AG. NucleoSpin ist ein eingetragenes Warenzeichen der Machery Nagel GmbH & Co. KG. QIAamp ist ein eingetragenes Warenzeichen der Qiagen GmbH. ZR Fungal/Bacterial DNA MiniPrep TM ist ein eingetragenes Warenzeichen der Zymo Research Corporation. Es kann nicht davon ausgegangen werden, dass die in diesem Handbuch verwendeten Markennamen oder Warenzeichen ungeschützt sind, auch wenn sie nicht als Markenname oder Warenzeichen gekennzeichnet sind Biotype Diagnostic GmbH, alle Rechte vorbehalten.
4 4 Inhaltsverzeichnis 1. Symbole Kit-Inhalt Lagerung Qualitätssicherung Anwendungsgebiet Sicherheitsinformationen Einleitung Produktbeschreibung Übersicht der notwendigen Arbeitsschritte Vom Anwender bereitzustellende Ausrüstung und zusätzlich benötigte Reagenzien Wichtige Hinweise Wichtige Hinweise vor Präparationsbeginn Probennahme und -versand Protokolle Lyse der Patientenproben mit anschließender DNA-Isolierung PCR-Amplifikation Agarosegelelektrophorese Auswertung Troubleshooting PCR-Amplifikation Gelelektrophorese Fehler in der Gelfärbung Referenzen... 27
5 5 1. Symbole Hersteller Herstellungsdatum Chargenbezeichnung 50 Inhalt ausreichend für 50 Reaktionen Gebrauchsanweisung beachten Verwendbar bis Temperaturbegrenzung Bestellnummer In-vitro-Diagnostika
6 6 2. Kit-Inhalt Mentype MycoDerm QS PCR-Amplifikationskit Bestellnummer Anzahl der Reaktionen 50 Nuklease-freies Wasser / Nuclease-free Water Reaktionsmix / Reaction Mix D (REM D) Multi Taq2 DNA-Polymerase / Multi Taq2 DNA-Polymerase Primergemisch / Primermix PCR 1 Kontroll-DNA / Control-DNA PCR 1 (2 ng/μl) (Microsporum gypseum) QS Sensor / Quality Sensor PCR 1 Referenzleiter / Reference Ladder PCR 1 Primergemisch / Primermix PCR 2 Kontroll-DNA / Control-DNA PCR 2 (2 ng/μl) (Trichophyton rubrum) QS Sensor / Quality Sensor PCR 2 Referenzleiter / Reference Ladder PCR 2 Puffer L / Buffer L (conc.)* Puffer N / Buffer N 2 x 1,9 ml 1 x 500 μl 1 x 40 μl 1 x 10 μl 50 μl 10 μl 50 μl 80 μl 50 μl 10 μl 50 μl 80 μl 3 x 0,6 ml 3 x 1,5 ml *Resuspendieren Sie den Röhrcheninhalt in einem Volumen von 1,4 ml Nuklease-freiem Wasser. 3. Lagerung Die Lagerung der PCR-Reagenzien (REM D, Taq2, Primer, H 2 0) sowie der Standards (Referenzleiter, Kontroll-DNA und Quality Sensor (QS)) über einen längeren Zeitraum sollte bei -20 C erfolgen. Wiederholtes Auftauen und Einfrieren sollte vermieden werden. Der Puffer L und der Puffer N können bei Raumtemperatur aufbewahrt werden. Die Referenzleitern sowie die Kontroll- DNA der PCR 1 und PCR 2 müssen unbedingt getrennt von den PCR- Reagenzien gelagert werden (Trennung der Bereiche Prä- und Post-PCR zur Vermeidung von Kontaminationen). Die Haltbarkeit des Testkits ist auf dem Verpackungsetikett angegeben. 4. Qualitätssicherung Die Herstellung der Biotype Diagnostic GmbH ist gemäß DIN EN ISO 9001: 2008 zertifiziert. Die Qualität der Testkits wird kontinuierlich auf vorher festgelegte Spezifikationen überprüft, um die uneingeschränkte Verwendbarkeit zu belegen. Bitte kontaktieren Sie uns in allen Fragen zur Qualitätssicherung unter support@biotype.de.
7 7 5. Anwendungsgebiet Das Mentype MycoDerm QS Kit ist ein vollwertiges In-vitro-Diagnostikum (IVD) zum Direktnachweis von Dermatophyten, Hefen und Schimmelpilzen in klinischen Proben bei Verdacht auf Dermatomykose. Als Proben eignen sich Nagelmaterial und Hautschuppen, aber auch Haarstümpfe oder Abstriche. Mit dem Kit wurden umfangreiche Validierungen, einschließlich einer klinischen Leistungsbewertung gemäß der Anforderungen der In-Vitro Diagnostics Directive 98/79/EC (IVDD), durchgeführt. Eine Konformitätserklärung wurde erstellt und das Kit als CE-IVD durch die zuständige Behörde unter DE/CA83/ registriert. Dieses Produkt ist für die Anwendung durch qualifiziertes Fachpersonal (wie etwa Labortechniker und Ärzte, die in molekularbiologischen Techniken geschult sind) bestimmt. Alle diagnostischen Ergebnisse, die durch Anwendung des Probenpräparationsverfahrens in Verbindung mit einem diagnostischen Test erzielt wurden, sind unter Berücksichtigung anderer klinischer Befunde oder Laborergebnisse auszuwerten. Um Abweichungen der diagnostischen Ergebnisse möglichst gering zu halten, sind geeignete Kontrollen mitzuführen. 6. Sicherheitsinformationen Tragen Sie beim Umgang mit Chemikalien immer einen Laborkittel, Schutzhandschuhe und eine Schutzbrille. Für alle Kitkomponenten können die Sicherheitsdatenblätter bei der Biotype Diagnostic GmbH angefordert werden. Für Sicherheitsdatenblätter von Reagenzien, die nicht im Testkit enthalten sind, kontaktieren Sie bitte den jeweiligen Hersteller. Folgende potenziell gefährliche Substanzen sind in diesem Testkit enthalten: Kitbestandteil Chemikalie Anteil Gefährdungen (H) und Vorsichtsmaßnahmen (P) Buffer L (conc.) KOH 10 % GHS05: Gefahr Ätzwirkung // H302 (Gesundheitsschädlich beim Verschlucken), H314 (verursacht schwere Verätzungen der Haut und schwere Augenschäden), GHS07 Achtung! // H290 (kann gegenüber Metallen korrosiv sein) P280 (Schutzhandschuhe / Schutzkleidung / Augenschutz / Gesichtsschutz tragen), P (bei Verschlucken Mund mit Wasser ausspülen, kein Erbrechen herbeiführen), P (bei Kontakt mit den Augen einige Minuten lang behutsam mit Wasser spülen. Kontaktlinsen nach Möglichkeit entfernen; weiter ausspülen), P309+P310 (bei Exposition oder Unwohlsein sofort Giftinformationszentrum oder Arzt anrufen)
8 8 7. Einleitung 7.1 Produktbeschreibung Das Mentype MycoDerm QS PCR-Amplifikationskit erlaubt die effiziente Diagnostik von Dermatomykosen (Hautpilzinfektionen) im Routinelabor. Diese molekularbiologische Diagnostik basiert auf der Amplifikation spezifischer DNA-Sequenzen, die in sogenannten Markergenbereichen der jeweiligen Dermatomykoseerreger lokalisiert sind und eine artspezifische Unterscheidung zulassen. Die Detektion erfolgt mittels Agarosegelelektrophorese mit anschließender Geldokumentation. Das Assay wurde so konzipiert, dass eine leicht handhabbare, routinefähige und sichere Diagnostik innerhalb von 24 Stunden ermöglicht wird. Dies steht im Gegensatz zu der sehr zeitaufwendigen klassischen Diagnostik von Dermatomykosen, die umfangreiche, bis zu vier Wochen andauernde Kultivierungen benötigt. Bedingt durch das Risiko von Probenkontaminationen (z. B. Anflugkeime) oder einer Unterdrückung des Hauptkeims durch einen schneller wachsenden Sekundärkeim in Mischproben erhöht die Kultivierung außerdem die Gefahr von Fehlinterpretationen. Diese potentiellen Fehlerquellen können durch die Anwendung des Mentype MycoDerm QS Assays ausgeschlossen werden. Das Assay beinhaltet optimierte Reagenzien für den art- bzw. gattungsspezifischen Nachweis von 21 in Europa relevanten Dermatophyten, Hefen und Schimmelpilzen [1]. Die Auswahl und Abgrenzung der Erreger (siehe Tabelle 1) wurde in Absprache mit klinischen Experten getroffen und trägt sowohl zur raschen Abklärung der Krankheitsursache als auch zur situationsgerechten Therapieentscheidung bei. Insbesondere ist dies vor dem Hintergrund zunehmender Antimykotikaresistenzen von großer Bedeutung [2, 3]. Gemäß den Qualitätsstandards in der mikrobiologisch-infektiologischen Diagnostik (MiQ) der Deutschen Gesellschaft für Hygiene und Mikrobiologie (DGHM) [4] enthält der Mentype MycoDerm QS eine interne PCR- Amplifikationskontrolle (Quality Sensor, QS). Im Falle eines negativen Erregernachweises (fehlendes Erreger-Amplifikat) dient diese als Bestätigung einer erfolgreich durchgeführten PCR. Zur raschen und sicheren Zuordnung der PCR-Produkte ist dem Kit eine sogenannte Referenzleiter beigefügt. Dabei handelt es sich um ein Gemisch von erregerspezifischen Amplifikationsprodukten für die unkomplizierte Zuordnung der Erregeramplifikate.
9 9 Tabelle 1: Dermatophyten, Hefen und Schimmelpilzerreger, nachweisbar in der kombinierten Multiplex-PCR des Mentype MycoDerm QS Assays Gattung Art Primertyp gattungsspezifisch erfasste Arten Epidermophyton floccosum artspezifisch Microsporum canis (1) artspezifisch Microsporum gypseum (2) artspezifisch Trichophyton rubrum artspezifisch Trichophyton interdigitale (3) artspezifisch Trichophyton spp. gattungsspezifisch T. rubrum T. interdigitale (3) T. tonsurans T. violaceum T. verrucosum Arthroderma benhamiae (4) Candida spp. gattungsspezifisch C. albicans C. tropicalis C. glabrata C. krusei (Pichia kudriavzevii, Issatchenkia orientalis) C. guilliermondii (Meyerozyma guilliermondii) C. parapsilosis Trichosporon cutaneum artspezifisch Scopulariopsis brevicaulis artspezifisch Aspergillus spp. gattungsspezifisch A. fumigatus A. flavus A. niger A. versicolor (1) teleomorph: Arthroderma otae, (2) teleomorph: Arthroderma gypseum, (3) teleomorph: Arthroderma vanbreuseghemii, (4) anamorph: Trichophyton erinacei
10 Übersicht der notwendigen Arbeitsschritte Arbeitszeit Arbeitszeit Arbeitsablauf Wartezeit Wartezeit 15 min 15 min Proben - Lyse =12 h > 12 h 2 h 2 h DNA - Extraktion * min min Ansetzen Mastermix Mastermix Mastermix PCR 1 PCR 2 Multiplex-PCR h 2-2,5 h 15 min 15 min Agarose-Gel gießen Agarose-Gel aushärten 30 min 30 min 30 min 30 min Agarose-Gel beladen Gel - Eletrophorese 1 h 1 h 10 min 10 min Gel-Red TM Färbung 45 min 1 h 20 min 20 min Auswertung 4 h 4 h ca.15 ca. h 15 h Abbildung 1: Von der Probe bis zum Nachweis Diagnostik bei Verdacht auf Dermatomykosen mit Hilfe des Mentype MycoDerm QS PCR-Amplifikationskits. *Die Zeitangabe bezieht sich auf einen Ansatz mit 20 Proben.
11 11 8. Vom Anwender bereitzustellende Ausrüstung und zusätzlich benötigte Reagenzien Tragen Sie beim Umgang mit Chemikalien immer einen Laborkittel, Schutzhandschuhe und eine Schutzbrille. Weitere Informationen können Sie den entsprechenden Sicherheits-Datenblättern entnehmen, die beim jeweiligen Produktlieferanten erhältlich sind. Für die Probenaufbereitung und Amplifikation: Pipetten* und Pipettenspitzen (zur Vermeidung von Kreuzkontaminationen empfehlen wir die Verwendung von Pipettenspitzen mit Aerosolbarriere) Einmalhandschuhe (puderfrei) Heizblock* zur Lyse der Proben (z. B. den Eppendorf Thermomixer comfort mit einem Thermoblock für 1,5 ml Mikroreaktionsgefäße) # Mikro- und Minizentrifuge* Vortexer Thermocycler mit einer Heizrate von mind. 4-6 C # Außerdem werden folgende Reagenzien benötigt: Reagenz Anbieter # Bestellnummer DNA Isolations QIAamp DNA Mini Kit oder NucleoSpin Tissue Kit Ethanol % Qiagen GmbH Macherey-Nagel Carl Roth Für die Gelelektrophorese: Pipetten* und Pipettenspitzen Einmalhandschuhe (puderfrei) Heizrührer bzw. Mikrowelle Elektrophoresesystem (wir empfehlen das imupid Mini Agarose Gel Electrophoresis System von Helixx Technologies Inc.) # Färbeschale Geldokumentation (z. B. BioVision 3000 von Vilber Lourmat Deutschland GmbH) # Densitometrische Auswertesoftware (z. B. Bio-1D advanced von Vilber Lourmat Deutschland GmbH) # *Um die sachgemäße Verarbeitung der Proben im Rahmen des Kits zu gewährleisten, empfehlen wir, die Geräte (z. B. Pipetten und Heizblöcke) gemäß den Empfehlungen des jeweiligen Herstellers zu kalibrieren. # Dies ist keine vollständige Lieferantenliste; viele wichtige Laborbedarf-Vertreiber sind nicht aufgeführt.
12 12 Außerdem werden folgende Reagenzien benötigt: Reagenz Anbieter # Bestellnummer 6x Gelladepuffer für die DNA-Gelelektrophorese mit Bromphenolblau und Ficoll 400 Applichem GmbH A2572 GelRed (DNA-spezifischer Fluoreszenzfarbstoff) für die DNA- Biotium Inc Gelelektrophorese Agarose für die DNA-Gelelektrophorese PeqLab Biotechnologie GmbH TBE-Puffer für die DNA-Gelelektrophorese Applichem GmbH A0972 1x TE-Puffer Applichem GmbH A M Natriumchlorid-Lösung Applichem GmbH A3511 Wasser für die Molekularbiologie (Nuklease-frei) Applichem GmbH A7398 # Dies ist keine vollständige Lieferantenliste; viele wichtige Laborbedarf-Vertreiber sind nicht aufgeführt. 9. Wichtige Hinweise 9.1 Wichtige Hinweise vor Präparationsbeginn Überprüfen Sie die Kit-Komponenten nach Erhalt des Kits auf Beschädigungen. Bei Beschädigungen der Puffergefäße wenden Sie sich an den Technischen Service der Biotype Diagnostic GmbH oder Ihren Lieferanten. Im Falle von ausgelaufener Flüssigkeit lesen Sie bitte unter "Sicherheitsinformationen" (Seite 6) nach. Verwenden Sie keine beschädigten Kit-Komponenten, da die Leistungsfähigkeit des Kits dadurch beeinträchtigt werden könnte. Wechseln Sie nach jedem Pipettierschritt die Pipettenspitzen. Als Schutz vor Kreuzkontaminationen empfehlen wir die Verwendung von Pipettenspitzen mit Aerosolbarriere. Sämtliche Zentrifugationsschritte sind bei Raumtemperatur (15 25 C) durchzuführen. Tragen Sie stets Einmalhandschuhe und überprüfen Sie regelmäßig, ob sie nicht mit Probenmaterial kontaminiert sind (ggf. wechseln). Entsorgen Sie die Handschuhe, falls sie kontaminiert wurden. Öffnen Sie immer nur ein Gefäß, um Kreuzkontaminationen zu vermeiden. Kombinieren Sie nicht die Komponenten verschiedener Kits miteinander, es sei denn, die Chargennummern sind identisch. Vermeiden Sie eine mikrobielle Kontamination der Kit-Reagenzien. Um das Risiko einer Infektion durch potenziell infektiöses Material so gering wie möglich zu halten, empfehlen wir, bis zur Lyse der Proben unter einer Sterilbank zu arbeiten. Dieses Kit sollte nur von Personal verwendet werden, das in Verfahren der In-vitro-Labordiagnostik und der PCR-Methodik geschult ist.
13 Probennahme und -versand Generell erfolgt die Probenentnahme unter sterilen Bedingungen. Auf geeignete Arbeitsschutzmaßnahmen im Umgang mit potentiell infektiösen Patientenproben ist zu achten. Die geltenden Versandvorschriften für medizinisches Untersuchungsgut, das Krankheitserreger der Risikogruppe 2 enthalten kann, ist einzuhalten. Achtung! Die Probengewinnung sollte vor Therapiebeginn bzw. nach einer Therapiepause erfolgen (bisherige topische Behandlung mit Externa vor Verwendung des Kits beenden bzw. für 2-3 Wochen unterbrechen). Desinfektion: Da sich auf Haut, Nägeln und Haaren nicht pathogene Anflugkeime befinden können, sollte vor Probenentnahme eine gründliche Säuberung und Desinfektion des mykoseverdächtigen Herdes mit einem Tupfer und 70 %igem Ethanol erfolgen (Reduktion der kontaminierenden Begleitflora). Materialmenge: Nach Trocknung der desinfizierten Stelle sollte ausreichend Material entnommen werden, da Pilze nesterweise auftreten. Es sollte immer Material in der Nähe der Wachstumszone der Pilze entnommen werden (Grenzfläche zwischen mykotischer Veränderung und gesundem Haut- bzw. Nagelareal). Im Gegensatz zur klassischen Pilzdiagnostik, welche die Gewinnung lebenden Pilzmaterials voraussetzt, sind für den molekulargenetischen Nachweis zusätzlich auch gröbere Hautschuppenauflagerungen, Borken, Krusten und Nagelspäne ohne vitale Pilzelemente geeignet. Auch dieses Material enthält noch deutliche Mengen an nachweisbarem Erbmaterial. Technik: Zur Materialentnahme von infektiösen Hautpartien werden Schuppen in Richtung der Pilzwachstumszone mit einem sterilen Skalpell, einer Kürette oder einem scharfen Löffel entnommen. Bei Onychomykosen gilt, je feinspäniger das Material, desto erfolgreicher die Ausbeute an pilzlicher DNA. Leicht ablösbare bröcklige Teile sollten entfernt (Nagel ggf. mit Schere kürzen) und verworfen werden. Das Material (Nagelspäne) muss aus den befallenen Arealen der Nagelplatte, am Übergang vom "kranken" zum "gesunden" Gewebe, abgetragen werden. Tiefere Nagelpartien nahe dem Nagelbett und subunguale Hyperkeratosen sollten mit einbezogen werden. Bei der weißen superfiziellen Onychomykose muss das Material durch Abkratzen oder Fräsen der weißen Flecken gewonnen werden. Bei der Entnahme von Haaren sollten vorhandene Eiterkrusten vorsichtig entfernt und die Haare auf ca. 3-5 mm Länge gekürzt werden. Die abgeschnittenen Haare werden verworfen. Danach Haarstümpfe mit der Epilationspinzette entnehmen (Haarwurzeln müssen vorhanden sein!). Falls notwendig sollten die Haarstümpfe "ausgegraben" werden. Bereiche mit auffälligen Haaren, z. B. grau, entfärbt, glanzlos, weißliche Hülle oder abgebrochen, bevorzug beproben.
14 14 Für die Aufnahme und den Versand des entnommenen Materials empfehlen wir Sampletype i-sep SQ CE-IVD (Biotype Diagnostic GmbH; Bestellnummer ) zum Probentransport und zur Durchführung der Lyse zur Gewinnung eines partikelfreien DNA Lysates. Dafür wird die gewonnene Patientenprobe mit einem mit sterilen Wasser angefeuchteten, geflockten Tupfer (Regular Nylon Flocked Dry Swab; 3520CS01; Copan Diagnostics Inc., US) aufgenommen und in den Filtereinsatz des Kombigefäßes überführt. Der Versand in das Labor erfolgt trocken und bei Raumtemperatur. Alternativ eignen sich für den Probentransport auch sterile DNA-freie 1,5 ml Standardzentrifugenröhrchen. Hinweis! Bitte verwenden Sie für die Probenaufnahme keine Wattetupfer. Bei nässenden oder eitrigen Infektionsherden empfiehlt sich in der Praxis besonders das Abstrichbesteck Regular Nylon Flocked Dry Swab in Tube mit Patientenlabel der Firma Copan Innovation Inc. (Brescia, Italien; Bestellnummer 519C oder 552C; Vertrieb in Deutschland über Mast Diagnostica, Reinfeld). Die Probenentnahme sollte mit sanftem Andruck und mehrmaligem Drehen des Nylontupfers in beiden Richtungen erfolgen. Nach Beprobung den Tupfer zurück in das Probenröhrchen überführen und bei Raumtemperatur trocken in das Labor versenden. 10. Protokolle 10.1 Lyse der Patientenproben mit anschließender DNA-Isolierung Lyse von Haut- und Haarproben Für die Isolierung und Aufreinigung der DNA aus Haut- und Haarproben sollten stets DNA-Isolierungskits, die auf der Silikamembran-Technologie basieren, verwendet werden. Für die Probenlyse bzw. die DNA-Extraktion ist dabei nach den Angaben und Empfehlungen der jeweiligen Hersteller vorzugehen. Um einen optimalen Gewebeaufschluss zu gewährleisten, empfehlen wir generell die Inkubation mit Proteinase K über Nacht oder für mindestens 12 Stunden Lyse von Haut- und Haarproben unter Verwendung von Sampletype i-sep SQ CE-IVD Zur Vorbereitung des Lysepuffers werden pro Probe 180 μl ATL Puffer (Qiagen) bzw. 180 μl T1 Puffer (Macherey-Nagel) und 20 μl bzw. 25 μl Proteinase K gemischt. Pro Ansatz werden 5 % Überschuss kalkuliert, um Pipettierfehler zu kompensieren. Den resultierenden Puffer umgehend weiterverwenden.
15 15 Lyse der Probe: 200 μl Lysepuffer (vorgewärmt auf 56 C) werden zum Probenmaterial in den Filtereinsatz gegeben und das Kombigefäß wird mit dem Deckel verschlossen. Im Thermoschüttler bei 56 C und 850 U/min (oder alternative im Brutschrank bei 56 C) wird die Probe für wenigstens 12 Stunden inkubiert. Kondenstropfen im Deckel durch Zentrifugieren für 1 min bei max. 500 U/min entfernen. 200 μl Puffer AL (Qiagen) bzw. 200 μl Puffer B3 (Macherey-Nagel) zugeben und das Kombigefäß mit dem Deckel verschließen. Im Thermoschüttler bei 70 C und 850 U/min wird die Probe für 10 min inkubiert. Das Sampletype Kombigefäß wird für 1 min bei U/min zentrifugiert. Das Auffanggefäß wird verschlossen, nachdem der Filtereinsatz entfernt und verworfen wurde. Im Auffanggefäß befinden sich 400 μl Lysat, das die DNA der Dermatomykoseerreger aus der Probe enthält. Die weitere DNA-Aufreinigung erfolgt nach den Vorgaben des Herstellers des jeweiligen DNA-Isolierungskits (siehe10.1.5) Lyse von Nagelproben Zur effektiveren Aufarbeitung von Nagelproben empfehlen wir die Verwendung des Puffers L und des Puffers N, die dem Mentype MycoDerm QS Kit beiliegen. Dieser Lyseschritt wurde in Kombination mit dem QIAamp DNA Mini Kit und dem NucleoSpin Tissue Kit validiert. Dabei wird der erste kitspezifische Puffer (ATL bzw. T1) des DNA-Isolierungskits durch den Puffer L ersetzt. Vor dem ersten Gebrauch ist das Konzentrat des Puffers L mit jeweils 1,4 ml Nuklease-freiem Wasser (nicht im Kit enthalten) auf die Gebrauchskonzentration einzustellen. Die Puffer L und N sollten bei Verwendung Raumtemperatur haben. Die Probe in einem 1,5 ml Reaktionsgefäß (nicht Bestandteil des Kits) wird mit 100 μl Puffer L überschichtet. Es folgt eine Inkubation in einem Thermomixer (Heizblock) bei 90 C und U/min für 15 min. Anschließend werden die Proben unter 56 C abgekühlt und kurz zentrifugiert (1 min, >1000 U/min), um Flüssigkeitstropfen aus der Deckelinnenseite zu entfernen. Danach werden 80 μl Puffer N und 20 μl (Qiagen) bzw. 25 μl
16 16 (Macherey-Nagel) der Proteinase K-Lösung des jeweiligen DNA-Extraktionskits dazu pipettiert, gemischt und bei 56 C über Nacht ( mindestens 12 h) inkubiert. Die weitere DNA-Aufreinigung erfolgt nach den Vorgaben des Herstellers des jeweiligen DNA-Isolierungskits (siehe ) Lyse von Nagelproben unter Verwendung von Sampletype i-sep SQ CE-IVD Zur effektiveren Aufarbeitung von Nagelproben empfehlen wir die Verwendung des Puffers L und des Puffers N, die dem Mentype MycoDerm QS Kit beiliegen. Dieser Lyseschritt wurde in Kombination mit dem QIAamp DNA Mini Kit und dem NucleoSpin Tissue Kit validiert. Dabei wird der erste kitspezifische Puffer (ATL bzw. T1) des DNA-Isolierungskits durch den Puffer L ersetzt. Vor dem ersten Gebrauch ist das Konzentrat des Puffers L mit jeweils 1,4 ml Nuklease-freiem Wasser (nicht im Kit enthalten) auf die Gebrauchskonzentration einzustellen. Die Puffer L und N sollten bei Verwendung Raumtemperatur haben. Lyse der Probe: 100 μl Puffer L werden zum Probenmaterial in den Filtereinsatz gegeben und das Kombigefäß wird mit dem Deckel verschlossen. Im Thermomixer bei 90 C und U/min wird die Probe für 15 min inkubiert. Anschließend werden die Proben unter 56 C abgekühlt Kondenstropfen im Deckel durch Zentrifugieren für 1 min bei max. 500 U/min entfernen. 80 μl Puffer N und 20 μl (Qiagen) bzw. 25 μl (Macherey-Nagel) der Proteinase K-Lösung des jeweiligen DNA-Extraktionskits zugeben, mischen und das Kombigefäß mit dem Deckel verschließen. Im Thermoschüttler bei 56 C und 850 U/min wird die Probe über Nacht (mindestens 12 h) inkubiert. 200 μl Puffer AL (Qiagen) bzw. 200 μl Puffer B3 (Macherey-Nagel) zugeben und das Kombigefäß mit dem Deckel verschließen. Im Thermoschüttler bei 70 C und 850 U/min wird die Probe für 10 min inkubiert. Das Sampletype Kombigefäß wird für 1 min bei U/min zentrifugiert. Das Auffanggefäß wird verschlossen, nachdem der Filtereinsatz entfernt und verworfen wurde. Im Auffanggefäß befinden sich 400 μl Lysat, das die DNA der Dermatomykoseerreger aus der Probe enthält. Die weitere DNA-Aufreinigung
17 17 erfolgt nach den Vorgaben des Herstellers des jeweiligen DNA-Isolierungskits (siehe10.1.5) DNA-Aufreinigung Für die Aufreinigung der DNA sollten stets DNA-Isolierungskits, die auf der Silikamembran-Technologie basieren, verwendet werden. Dabei ist nach Angaben des jeweiligen Herstellers zu verfahren. Abweichend davon, sollte beim Elutionsschritt das Volumen des Elutionspuffers von zumeist 200 μl auf 50 μl reduziert werden. Das so gewonnene DNA-Isolat kann direkt für die PCR-Amplifikation verwendet werden PCR-Amplifikation Ansatz der Mastermixe Hinweis: Alle Reagenzien sollten so kurz wie möglich bei Raumtemperatur gehalten und nach der Verwendung sofort wieder bei -20 C gelagert werden. Der QS sollte zudem immer auf Eis pipettiert werden! Vor der Verwendung sollten die Reagenzien gut gemischt (vortexen) und kurz zentrifugiert werden (10 s). Die folgende Tabelle zeigt die Volumina der eingesetzten Kitbestandteile für den Ansatz PCR 1; 4 μl empfohlenes Probenvolumen (Template-DNA) in einem Reaktionsvolumen von 25 μl. Berücksichtigen Sie bei der Berechnung der Anzahl der PCR-Reaktionen die Positiv- und Negativkontrolle. Fügen Sie zu dieser Zahl ein oder zwei Reaktionen hinzu, um Pipettierfehler zu kompensieren. Komponente Nuclease-free Water Reaction Mix D* Primer Mix PCR 1 QS Sensor PCR 1 Multi Taq2 DNA-Polymerase (hot start, 2.5 U/μl) Volumen des Mastermixes *enthält Mg 2+, dntps, BSA Volumen 13,5 μl 5,0 μl 1,0 μl 1,0 μl 0,5 μl 21,0 μl
18 18 Die folgende Tabelle zeigt die Volumina der eingesetzten Kitbestandteile für den Ansatz PCR 2; 4 μl empfohlenes Probenvolumen (Template-DNA) in einem Reaktionsvolumen von 25 μl. Der QS Sensor muss vor der Präparation des Mastermixes immer frisch in 1x TE Puffer verdünnt werden (Verdünnungsfaktor 1:200). Berücksichtigen Sie bei der Berechnung der Anzahl der PCR-Reaktionen die Positiv- und Negativkontrolle. Fügen Sie zu dieser Zahl ein oder zwei Reaktionen hinzu, um Pipettierfehler zu kompensieren. Komponente Nuclease-free Water Reaction Mix D* Primer Mix PCR 2 QS Sensor PCR 2 (1:200) Multi Taq2 DNA-Polymerase (hot start, 2.5 U/μl) Volumen des Mastermixes *enthält Mg 2+, dntps, BSA Volumen 13,5 μl 5,0 μl 1,0 μl 1,0 μl 0,5 μl 21,0 μl Die PCR 1 zeigt ideale Ergebnisse bei Einsatz von 50 pg bis 250 pg Erreger- DNA und die PCR 2 bei 25 pg bis 100 pg Erreger-DNA. Bei Referenzmaterial und Isolaten von Kulturplatten ist der Einsatz von 1 μl DNA-Isolat (verdünnen auf 250 bzw. 100 pg/μl) meist völlig ausreichend. Bei Patientenmaterial empfehlen wir das optimale Volumen von 4 μl DNA-Isolat zu verwenden. Bei Verwendung anderer DNA-Probenvolumina muss das Volumen mit Nuklease-freiem Wasser entsprechend angepasst werden, so dass das Volumen des PCR-Ansatzes 25 μl beträgt. Die Gesamt-DNA pro PCR-Ansatz (humane DNA und ggf. Erreger-DNA) sollte 200 ng nicht übersteigen. Das Primergemisch ist so eingestellt, dass bei 40 PCR-Zyklen in einem Reaktionsvolumen von 25 μl ausreichend DNA für sichtbare Gelbanden amplifiziert wird Positivkontrollen Um die maximale Sensitivität des Assays zu gewährleisten, wird das Mitführen einer niedrig konzentrierten Positivkontrolle in beiden PCR-Ansätzen empfohlen. Verdünnen Sie hierfür die Kontroll-DNA PCR 1 bzw. PCR 2 (beide 2 ng/μl) auf 10 pg/μl (Verdünnungsfaktor 1:200). Pipettieren Sie 1 μl verdünnte Kontroll-DNA anstelle der Template-DNA in die Reaktionsgefäße mit dem vorgelegten PCR-Mastermix und füllen Sie das restliche Volumen bis 25 μl mit Nuklease-freiem Wasser auf.
19 19 Die Agarosegelelektrophorese ist optimal abgelaufen (Auftrennung, Färbung), wenn das resultierende PCR-Produkt anschließend sicher detektiert werden kann Negativkontrollen Als Negativkontrollen pipettieren Sie Nuklease-freies Wasser an Stelle der Template-DNA in die Reaktionsgefäße mit dem vorgelegten PCR-Mastermix für die Ansätze PCR 1 bzw. PCR 2. Hier sollte nach der Amplifikation neben der QS-Bande kein weiteres Amplifikat detektiert werden PCR-Amplifikationsparameter Beide Ansätze PCR 1 bzw. PCR 2 werden parallel unter gleichen PCR- Bedingungen amplifiziert. Um die Multi Taq2 DNA-Polymerase zu aktivieren und die Bildung von unspezifischen Amplifikationsprodukten zu unterdrücken, sollte unbedingt ein hot start durchgeführt werden. Temperatur Zeit 94 C 4 min (hot start für Aktivierung der Multi Taq2 DNA- Polymerase) 94 C 30 s 62 C 60 s 5 Zyklen 72 C 90 s 94 C 30 s 60 C 60 s 35 Zyklen 72 C 90 s 10 C bis zum Ende Zur Durchführung der PCR-Amplifikation sollte immer ein Thermocycler mit einer Heizrate von mind. 4-6 C/s zum Einsatz kommen. Die Validierung des Testkits wurde mit dem Mastercycler ep gradient S (Eppendorf AG) sowie dem Biometra T1 (Biometra GmbH) durchgeführt Agarosegelelektrophorese Prinzipiell sind für die Auswertung der Multiplex-PCR verschiedene Geräte für Gelelektrophorese und -dokumentation geeignet. Entscheidend für die Auflösung der erregerspezifischen Banden sind die Qualität und Konzentration der Agarose, die Dicke des Agarosegels (4-5 mm) sowie die Trennstrecke.
20 20 Für die Sensitivität sind die Schichtdicke des Gels, die DNA-Färbetechnik und der optische Aufbau des verwendeten Geldokumentationssystems entscheidend. Die dem Kit beiliegende Referenzleiter bzw. eine Kontroll-PCR unter Verwendung der ebenfalls beiliegenden Positivkontrolle kann zur Kalibrierung hauseigener Systeme genutzt werden. Grundlagen der Agarosegelelektrophorese entnehmen Sie Sambrook et al [5] bzw. folgen Sie den Anweisungen der Gerätehersteller. Die Validierung des Testkits wurde mit dem Elektrophoresesystem imupid Mini Agarose Gel Electrophoresis System (Helixx Technologies Inc.) in Kombination mit der Geldokumentation BioVision 3000 (Vilber Lourmat Deutschland GmbH) durchgeführt. Letztere verfügt über einen UV-Leuchttisch mit 312 nm Anregungswellenlänge und einem Emissionsfilter von 590 nm. Die Kamera wurde mit Blende 2,8 und Belichtungszeit 1-3 s eingestellt. Die Färbung erfolgte mit dem DNA-Farbstoff GelRed (Biotium Inc). Die Auswertung der Gelbilder erfolgte mit der Software Bio-1D advanced (Vilber Lourmat Deutschland GmbH) Probenvorbereitung Für ein Auftragsvolumen von 12 μl pro Geltasche werden 10 μl PCR-Probe und 2 μl 6x Gelladepuffer (Bromphenolblau und Ficoll 400) gut gemischt und das gesamte Volumen aufgetragen. Für die Verwendung der Referenzleiter werden 5 μl Referenzleiter und 5 μl 6x Gelladepuffer gemischt und das gesamte Volumen aufgetragen. Bei Gelen bis zu 12 Proben empfehlen wir zwei Referenzleitern pro Gel (beide Außentaschen). Bei größeren Gelen mit mehr als 12 Proben sollte zusätzlich eine Tasche in der Mitte des Gels mit der Referenzleiter beladen werden. Dies erleichtert die spätere Zuordnung der Produktbanden Elektrophorese Für die elektrophoretische Auftrennung wird ein 2 %iges Agarosegel in 1x TBE-Puffer benötigt (z.b. peqgold Universal-Agarose, PeqLab Biotechnologie GmbH oder vergleichbare Qualität). Die Geldicke sollte maximal 5 mm betragen. Gemäß Gerätehersteller wird die Elektrophorese bei 6 Volt/cm bezogen auf den Elektrodenabstand und bei Raumtemperatur (maximal 26 C) durchgeführt. Die Trennstrecke, dass heißt die Entfernung der Lauffront von den Auftragstaschen, sollte mindestens 5,5 cm betragen. Diese wird anhand des Bromphenolblau im Ladepuffer ersichtlich (Farbstoff zur Verfolgung der Laufweite).
21 DNA-Färbung mit GelRed TM und Geldokumentation Zur DNA-Färbung muss der Fluoreszenzfarbstoff GelRed TM (Biotium Inc.) verwendet werden, der bei der Validierung des Testkits eingesetzt wurde. Der Farbstoff besitzt vergleichbare spektrale Eigenschaften wie Ethidiumbromid, ist jedoch im Gegensatz dazu in der DNA-Färbung empfindlicher und im Hinblick auf Gesundheit und damit Arbeits- und Umweltschutzmaßnahmen unbedenklich [6]. Das Gel muss während des Färbens komplett vom Färbebad bedeckt sein. Für ein 3fach konzentriertes Gelfärbebad von 50 ml werden 15 μl GelRed TM Nucleic Acid Gel Stain x in Water (Biotium Inc.) mit 45 ml destilliertem Wasser und 5 ml 1 M NaCl-Lösung verdünnt. Um eine hohe Sensitivität zu gewährleisten, sollte das Bad immer frisch hergestellt und für maximal 2-3 Gele benutzt werden. Farbstoff und Färbebad müssen stets vor Licht geschützt aufbewahrt werden. Die Färbedauer sollte mindestens 50 min betragen und lichtgeschützt erfolgen. Aufgrund des Interkalierungsverhaltens des Farbstoffs ist unbedingt davon abzuraten, den Farbstoff während des Gelgießens zuzusetzen, da dies sonst zu verändertem Laufverhalten auf Grund von Ladungsänderungen der doppelsträngigen DNA führt Auswertung Grundsätzlich empfehlen wir eine Software zur automatischen Auswertung der Agarosegelbilder. Diese werden von der jeweiligen Steuerungssoftware der Geldokumentationssysteme im Windows Bitmap-Format (bmp) oder Tagged Image File Format (Tiff) abgespeichert. Sie können außerdem anschließend mittels der Software Bio-1D advanced (Vilber Lourmat Deutschland GmbH) unter Beachtung der Herstellerangaben eine automatische Bandendetektion und Fragmentlängenanalyse vornehmen. Die dafür benötigten Fragmentlängen der Referenzleitern der PCR 1 bzw. PCR 2 können Sie der Tabelle 2 entnehmen. Durch die Auswertung mit automatischer Zuordnung der Gelbanden wird eine genaue und zuverlässige Unterscheidung der einzelnen Organismen gewährleistet. Ein erfolgreiches Experiment zeichnet sich durch eine sichtbare Bande des Quality Sensors (QS) in allen Reaktionen aus. Die Negativkontrolle sollte keine zusätzlichen Banden aufweisen 1. Die Sensitivität des Tests ist gewährleistet, wenn eine Bande der Positivkontrolle mit 10 pg sicher detektiert werden kann (siehe Positivkontrolle S. 17). 1 Bei hohen Konzentrationen erregerspezifischer DNA und deren Amplifikaten kann die QS-Bande teilweise unterdrückt werden.
22 22 Abbildung 2 zeigt beispielhaft ein Agarosegel mit den erregerspezifischen Amplifikaten des art- und gattungsspezifischen Nachweises der Dermatophyten, die in der PCR 1 erfasst werden. RL1 A B C D E F G NK RL1 QS QS: RL1: NK: A: B: C: D: E: F: G: Quality Sensor Referenzleiter PCR 1 Negativkontrolle Aspergillus spp. Microsporum canis Candida spp. Epidermophyton floccosum Trichosporon cutaneum Scopulariopsis brevicaulis Microsporum gypseum Abbildung 2: Gelelektrophorese PCR 1: 2 %iges Agarosegel; Trennstrecke: 7,0 cm; Elektrophoresebedingungen: 60 min bei 6 V/cm, Detektion: GelRed (Biotium, Inc.). Abbildung 3 zeigt beispielhaft ein Agarosegel mit den erregerspezifischen Amplifikaten des art- und gattungsspezifischen Nachweises der Dermatophyten, die in der PCR 2 erfasst werden. RL2 H I J NK RL2 QS QS: RL2: NK: H: I: J: Quality Sensor Referenzleiter PCR 2 Negativkontrolle Trichophyton interdigitale Trichophyton rubrum Trichophyton spp. Abbildung 3: Gelelektrophorese PCR 2: 2 %iges Agarosegel; Trennstrecke: 7,0 cm; Elektrophoresebedingungen: 60 min bei 6 V/cm, Detektion: GelRed (Biotium, Inc.).
23 23 Tabelle 2: Größe der einzelnen Banden des Mentype MycoDerm QS für die jeweiligen Dermatomykoseerreger in zwei parallelen PCR-Ansätzen. PCR 2 Parameter PCR 1 Bandengröße [bp] # Bandengröße [bp] # Aspergillus spp Microsporum canis Candida spp Epidermophyton floccosum Trichosporon cutaneum Scopulariopsis brevicaulis Microsporum gypseum Trichophyton interdigitale - 298* Trichophyton rubrum - 373* Trichophyton spp Quality Sensor (QS) # Durch das Laufverhalten der PCR-Amplifikate im Agarosegel kann es im Vergleich zu einem externen Längenstandard zu prozentualen Abweichungen von maximal 5 % der theoretischen Amplifikatgröße kommen. *Bei T. interdigitale und T. rubrum wird zusätzlich die Bande für Trichophyton spp. amplifiziert.
24 Troubleshooting 11.1 PCR-Amplifikation PCR-Produkt vorhanden, QS-Bande unterdrückt oder fehlt ganz: Stellen Sie sicher, dass die richtige QS-Verdünnung den einzelnen Ansätzen PCR 1 bzw. PCR 2 zugeordnet wurde. Ist eine spezifische Erreger-Bande detektierbar, ist davon auszugehen, dass die PCR funktioniert hat. Bei einem ungünstigen Konzentrationsverhältnis des QS und der Erreger-DNA kann auf Grund zu hoher Konzentration an Erreger- DNA in der PCR die Bande des Quality Sensors unterdrückt sein. Trichophyton spp. Bande und/oder QS-Bande unterdrückt oder fehlt ganz: Bei PCR 2 kann die Trichophyton spp. Bande ausfallen, wenn es sich um T. rubrum oder T. interdigitale handelt. Auch hier kann ein ungünstiges Konzentrationsverhältnis des QS zur Erreger-DNA zum Ausfall der QS-Bande führen. Weiterhin besteht eine Konkurrenz in der PCR-Amplifikation zwischen sog. single- und multicopy-genen, wobei kleinere Amplifikate bevorzugt vervielfältig werden, was zu einer sehr schwachen T. spp.-bande oder sogar zum Ausfall dieser führen kann. Keine Bande detektierbar, QS nicht vorhanden: Fehler im Setup: Überprüfen Sie, ob alle Reagenzien mit angegebenen Volumina und Konzentration zugegeben und die Lagerbedingungen der Reagenzien eingehalten wurden. Häufige Frieren-Tauen-Zyklen können negativen Einfluss auf die Stabilität der Reagenzien haben. Vor Beginn der PCR sollten die Reagenzien gut gemischt und abzentrifugiert werden. PCR mit neuem Reaktionsansatz wiederholen. Fehler des PCR-Gerätes (Amplifikation nicht erfolgt): Überprüfen Sie, ob das richtige PCR-Programm gewählt bzw. programmiert wurde. Überprüfen Sie die Funktionsfähigkeit des PCR-Gerätes. Verdunstung der Probe während der PCR (Augenprobe, ob Reaktionsansatz nach PCR noch Anfangsvolumen enthält): Deckelheizung muss aktiviert sein (105 ºC empfohlen).
25 25 Probleme der Gelelektrophorese und Gelfärbung: Siehe Problembehandlung Agarosegelelektrophorese weiter unten. Zusätzliche Banden, Bandengröße nicht korrekt, Bande in der Negativkontrolle: Reagenzien sind kontaminiert: Verwenden Sie immer frisch pipettierte Reaktionsansätze. Vergewissern Sie sich, dass die Pipetten nicht kontaminiert sind; diese sollten regelmäßig gesäubert/sterilisiert werden. Verwenden Sie Filterspitzen, um Kontaminationen zu vermeiden. Verwenden Sie je einen eigenen Pipettensatz für die Prä- und Post- PCR-Bearbeitung. Verschließen Sie nach Bearbeitung jeweils die einzelnen Reaktionsansätze. Wechseln Sie regelmäßig die Handschuhe. Konzentration an humaner DNA in der Probe ist zu hoch (Background): Stellen Sie bei der Probennahme sicher, dass hauptsächlich pilzliches Material entnommen wird. Überschuss und Zusammenschluss von unverbrauchten Primern können auftreten (Banden sind aber kleiner als 200 bp). Hinweis! Bitte bewahren Sie zur Kontaminationsvermeidung die Referenzleiter immer getrennt von den anderen Reagenzien auf Gelelektrophorese Atypische Banden, geringe Qualität der Banden (Smiley-Effekt, Doppelbanden, Schmier): Überprüfen Sie die Konzentration des Laufpuffers (empfohlen ist 1x TBE). Stellen Sie sicher, dass das Agarosegel die richtige Konzentration aufweist (optimale Konzentration 2 %). Die Trennstrecke ist für eine optimale Auflösung der Banden zu kurz gewählt (optimal 5-7 cm). Überhöhte Spannungen verursachen eine zu rasche Migration kleiner DNA-Fragmente, zu niedrige hingegen führen zu einer geringen Bandenschärfe; außerdem kann überhöhte Spannung zum Überhitzen oder Schmelzen des Agarosegels oder zur Denaturierung der DNA führen (optimale Einstellung 80 V bis 120 V, 5-8 V/cm); bei zu hohen Voltzahlen kann es zur Bildung von Doppelbanden kommen (optimale Einstellung 80 V bis 120 V, 5-8 V/cm).
26 26 Bei 5-8 V/cm sollte die Geldicke nicht mehr als 5 mm betragen Stellen Sie sicher, dass das Gel während der Elektrophorese immer vollständig mit Laufpuffer bedeckt ist. Vergewissern Sie sich, dass das Gel keine Luftblasen oder Fremdpartikel enthält; die Gele sollten stets langsam gegossen, entstandene Luftblasen ggf. mit der Pipette entfernt werden. Verwenden Sie beim Gießen des Gels stets saubere Gefäße (angetrocknete, alte Agaroserückstände beeinflussen den Gellauf negativ). Vergewissern Sie sich, dass die Agarose vor Beladen des Gels vollständig im Puffer gelöst ist (nicht gelöste/geschmolzene Agarose beeinflust den Gellauf negativ). Färbelösung (z.b. GelRed TM ), die bereits während der Gelelektrophorese zugegeben wird, stört den Gellauf und verursacht atypische DNA-Bandenmuster Fehler in der Gelfärbung Geringer Kontrast, schlechte bildliche Auflösung: Überprüfen Sie die Konzentration des Färbebades. Die GelRed TM Lösung ist zu alt bzw. wurde durch Licht geschädigt; stellen Sie sicher, dass das Färbebad lichtgeschützt aufgestellt und bereits angesetzte GelRed TM -Lösung lichtgeschützt gelagert wird. Das Agarosegel wurde zu dick gegossen (> 5 mm), die Konzentration des Färbebades ist nicht mehr ausreichend (bitte beachten Sie die Hinweise des Herstellers [7]). Färbelösung (z.b. GelRed TM ), die bereits während der Gelelektrophorese zugegeben wird, stört den Gellauf und verursacht atypische DNA-Bandenmuster.
27 Referenzen [1] Seebacher C, Bouchara JP, Mignon B. Updates on the epidemiology of dermatophyte infections. Mycopathologia 166, , [2] Seebacher C, Brasch J, Abeck D, Cornely O, Effendy I, Ginter- Hanselmayer G, Haake N, Hamm G, Hipler UC, Hof H, Korting HC, Mayser P, Ruhnke M, Schlacke KH, Tietz HJ; German Society of Dermatology; German-speaking Mycological Society. Onychomycosis. Mycoses 50, , [3] [4] Reischl U, Drosten C, Geißdörfer W, Göbel U, Hoffmann KS, Mauch H, Meyer T, Moter A, von Müller L, Panning M, Rabenau HF, Reiter-Owona I, Roth A, Weitz M. MiQ , Nukleinsäure-Amplifikationstechniken. In. Podbielski A, Hermann M, Kniehl E, Mauch H, Rüssmann H (Hrsg.) Mikrobiologisch-infektiologische Qualitätsstandards (MiQ). Im Auftrag der Deutschen Gesellschaft für Hygiene und Mikrobiologie (DGHM). 3. Auflage. Elsevier / Urban & Fischer, München, [5] Sambrook J, Fritsch EF, Maniatis T (Hrsg). Molecular Cloning: A Laboratory Manual. 2. Auflage. Cold Spring Harbor Laboratory Press, NY US, [6] Biotium Inc. Safety Report of GelRed and GelGreen - A Summary of Mutagenicity and Environmental Safety Test Results from Three Independent Laboratories, GG%20safety.pdf [7] GelRedTM Nucleic Acid Gel Stain Product protocol.
Mentype MycoDerm QS. Gebrauchsanleitung. Der schnelle und sichere Erregernachweis bei Verdacht auf Dermatomykosen
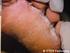 Mentype MycoDerm QS Gebrauchsanleitung Der schnelle und sichere Erregernachweis bei Verdacht auf Dermatomykosen Für In-vitro-diagnostische Untersuchungen 50 Made in Germany 45-21310-0050 Biotype Diagnostic
Mentype MycoDerm QS Gebrauchsanleitung Der schnelle und sichere Erregernachweis bei Verdacht auf Dermatomykosen Für In-vitro-diagnostische Untersuchungen 50 Made in Germany 45-21310-0050 Biotype Diagnostic
Mycoplasma gallisepticum
 BACTOTYPE PCR Amplification Kit Mycoplasma gallisepticum Labor Diagnostik Leipzig Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE PCR Amplification Kit umfasst optimierte Systeme zum Nachweis
BACTOTYPE PCR Amplification Kit Mycoplasma gallisepticum Labor Diagnostik Leipzig Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE PCR Amplification Kit umfasst optimierte Systeme zum Nachweis
Borrelia burgdorferi s.l.
 BACTOTYPE PCR Amplification Kit Borrelia burgdorferi s.l. Labor Diagnostik Leipzig Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE PCR Amplification Kit umfasst optimierte Systeme zum Nachweis
BACTOTYPE PCR Amplification Kit Borrelia burgdorferi s.l. Labor Diagnostik Leipzig Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE PCR Amplification Kit umfasst optimierte Systeme zum Nachweis
Mycobacterium paratuberculosis
 BACTOTYPE PCR Amplification Kit Mycobacterium paratuberculosis Labor Diagnostik Leipzig Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE PCR Amplification Kit umfasst optimierte Systeme zum Nachweis
BACTOTYPE PCR Amplification Kit Mycobacterium paratuberculosis Labor Diagnostik Leipzig Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE PCR Amplification Kit umfasst optimierte Systeme zum Nachweis
Chlamydia sp. BACTOTYPE PCR Amplification Kit. Gebrauchsanweisung. Labor Diagnostik Leipzig
 BACTOTYPE PCR Amplification Kit Chlamydia sp. Labor Diagnostik Leipzig Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE PCR Amplification Kit umfasst optimierte Systeme zum Nachweis von pathogenen
BACTOTYPE PCR Amplification Kit Chlamydia sp. Labor Diagnostik Leipzig Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE PCR Amplification Kit umfasst optimierte Systeme zum Nachweis von pathogenen
AdnaTest ER/PR-Detect
 PCR-Expressionsanalyse der Östrogen- und Progesteron- Hormonrezeptoren in angereicherten Tumorzellen Zur In-vitro-Diagnostik Gebrauchsanweisung T-1-532 Inhaltsverzeichnis Bestellinformation... 3 Anwendungszweck...
PCR-Expressionsanalyse der Östrogen- und Progesteron- Hormonrezeptoren in angereicherten Tumorzellen Zur In-vitro-Diagnostik Gebrauchsanweisung T-1-532 Inhaltsverzeichnis Bestellinformation... 3 Anwendungszweck...
SCRIPTUM HIGH PRECISE
 Nur für Forschungszwecke Datenblatt Artikel BS.50.020 = 20 Reaktionen x 50 µl Artikel BS.50.100 = 100 Reaktionen x 50 µl Artikel BS.50. 500 = 500 Reaktionen x 50 µl Haltbarkeit: 12 Monate Lagerung bei
Nur für Forschungszwecke Datenblatt Artikel BS.50.020 = 20 Reaktionen x 50 µl Artikel BS.50.100 = 100 Reaktionen x 50 µl Artikel BS.50. 500 = 500 Reaktionen x 50 µl Haltbarkeit: 12 Monate Lagerung bei
AdnaTest EMT-2/StemCell Add-on ProstateDetect
 AdnaTest EMT-2/StemCell Add-on ProstateDetect RT-PCR-Nachweis von Prostatakrebs-assoziierter Genexpression in angereicherten Tumorzellen Nur für Forschungszwecke Gebrauchsanweisung T-1-537-PP Inhaltsverzeichnis
AdnaTest EMT-2/StemCell Add-on ProstateDetect RT-PCR-Nachweis von Prostatakrebs-assoziierter Genexpression in angereicherten Tumorzellen Nur für Forschungszwecke Gebrauchsanweisung T-1-537-PP Inhaltsverzeichnis
RealLine DNA Extraction 2
 RealLine Pathogen Diagnostic Kits Gebrauchsinformation RealLine DNA Extraction 2 KIT FÜR DIE EXTRAKTION VON DNA AUS KLINISCHEN PROBEN In-vitro Diagnostikum RealLine DNA-Extraction 2 VBC8897 96 Tests gültig
RealLine Pathogen Diagnostic Kits Gebrauchsinformation RealLine DNA Extraction 2 KIT FÜR DIE EXTRAKTION VON DNA AUS KLINISCHEN PROBEN In-vitro Diagnostikum RealLine DNA-Extraction 2 VBC8897 96 Tests gültig
AdnaTest ColonCancerDetect
 AdnaTest ColonCancerDetect RT-PCR-Nachweis von Darmkrebs-assoziierter Genexpression in angereicherten Tumorzellen Zur In-vitro-Diagnostik Gebrauchsanweisung T-1-505 Inhaltsverzeichnis Bestellinformation...
AdnaTest ColonCancerDetect RT-PCR-Nachweis von Darmkrebs-assoziierter Genexpression in angereicherten Tumorzellen Zur In-vitro-Diagnostik Gebrauchsanweisung T-1-505 Inhaltsverzeichnis Bestellinformation...
Produktkatalog 2010. Molekularbiologische Reagenzien
 Produktion, Vertrieb und Serviceleistung im Bereich der Molekularbiologie und Medizin Produktkatalog 2010 Molekularbiologische Reagenzien Molegene GmbH Bienenweg 28 35764 Sinn Tel. 02772-570952 Fax 02772-570945
Produktion, Vertrieb und Serviceleistung im Bereich der Molekularbiologie und Medizin Produktkatalog 2010 Molekularbiologische Reagenzien Molegene GmbH Bienenweg 28 35764 Sinn Tel. 02772-570952 Fax 02772-570945
Inhaltsverzeichnis. Polymerase Chain Reaction Theoretischer Hintergrund - 2 -
 Inhaltsverzeichnis 1 Theoretischer Hintergrund - 2-1.1 Die Komponenten der PCR - 2-1.2 Das Verfahren der PCR - 3-1.3 Die Gelelektrophorese - 5-2 Material und Methoden - 6-3 Ergebnisse - 7-3.1 Ergebnisse
Inhaltsverzeichnis 1 Theoretischer Hintergrund - 2-1.1 Die Komponenten der PCR - 2-1.2 Das Verfahren der PCR - 3-1.3 Die Gelelektrophorese - 5-2 Material und Methoden - 6-3 Ergebnisse - 7-3.1 Ergebnisse
GVO-Screening Kit. Nachweis von gentechnischen Veränderungen mittels Polymerasekettenreaktion (PCR)
 GVO-Screening Kit Nachweis von gentechnischen Veränderungen mittels Polymerasekettenreaktion (PCR) I. Einführung Die Gentechnik stellt die Landwirtschaft vor neue Herausforderungen. Einerseits eröffnet
GVO-Screening Kit Nachweis von gentechnischen Veränderungen mittels Polymerasekettenreaktion (PCR) I. Einführung Die Gentechnik stellt die Landwirtschaft vor neue Herausforderungen. Einerseits eröffnet
chemagic Plasma D2.0 Kit
 chemagic Plasma D2.0 Kit (Art.-Nr. D-1047) Symbole 240 Kit enthält Reagenzien für 240 Isolierungen Informationen im Handbuch V081116 Verfallsdatum Chargennummer In-vitro Diagnostikum Temperaturbeschränkungen
chemagic Plasma D2.0 Kit (Art.-Nr. D-1047) Symbole 240 Kit enthält Reagenzien für 240 Isolierungen Informationen im Handbuch V081116 Verfallsdatum Chargennummer In-vitro Diagnostikum Temperaturbeschränkungen
Protokoll zur Übung PCR
 Protokoll zur Übung PCR im Rahmen des Praktikums Labor an der TU Wien Durchgeführt bei Ao.Univ.Prof. Mag. Dr.rer.nat. Robert Mach Verfasser des Protokolls: Gwendolin Korinek 0625083 & Daniel Bomze 0726183
Protokoll zur Übung PCR im Rahmen des Praktikums Labor an der TU Wien Durchgeführt bei Ao.Univ.Prof. Mag. Dr.rer.nat. Robert Mach Verfasser des Protokolls: Gwendolin Korinek 0625083 & Daniel Bomze 0726183
Haut und Nagelmaterial. Hautabstrich Hautbiopsie Hautgeschabsel, Hautschuppen Tesa-Abklatschpräparat der Haut Nagelspäne Haare.
 Haut und Nagelmaterial Hautabstrich Hautbiopsie Hautgeschabsel, Hautschuppen Tesa-Abklatschpräparat der Haut Nagelspäne Haare Hautabstrich Probengefäß Universalabstrichtupfer mit Transportmedium Materialentnahme
Haut und Nagelmaterial Hautabstrich Hautbiopsie Hautgeschabsel, Hautschuppen Tesa-Abklatschpräparat der Haut Nagelspäne Haare Hautabstrich Probengefäß Universalabstrichtupfer mit Transportmedium Materialentnahme
Protokoll Praktikum für Humanbiologie Studenten
 Protokoll Praktikum für Humanbiologie Studenten Teil A: Charakterisierung der Auswirkungen von γ Interferon auf die Protein und mrna Mengen in humanen A549 Lungenepithelzellen. Studentenaufgaben Tag 1
Protokoll Praktikum für Humanbiologie Studenten Teil A: Charakterisierung der Auswirkungen von γ Interferon auf die Protein und mrna Mengen in humanen A549 Lungenepithelzellen. Studentenaufgaben Tag 1
SERVALight EosUltra Western Blot Chemilumineszenz HRP Substrat Kit
 GEBRAUCHSANLEITUNG SERVALight EosUltra Western Blot Chemilumineszenz HRP Substrat Kit (Kat.-Nr. 42586) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010
GEBRAUCHSANLEITUNG SERVALight EosUltra Western Blot Chemilumineszenz HRP Substrat Kit (Kat.-Nr. 42586) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010
Nachweis von DNA im Wein
 Abschlussbericht über den Forschungsauftrag Nachweis von DNA im Wein Projektlaufzeit: 01.01.2001 bis 31.03.2003 Prof. Dr. Ralf Kaldenhoff Universität Würzburg Julius-von-Sachs-Institut für Biowissenschaften
Abschlussbericht über den Forschungsauftrag Nachweis von DNA im Wein Projektlaufzeit: 01.01.2001 bis 31.03.2003 Prof. Dr. Ralf Kaldenhoff Universität Würzburg Julius-von-Sachs-Institut für Biowissenschaften
Plasmidpräparation aus Bakterien Inhalt
 Inhalt Einleitung... 2 Materialien... 4 Gewinnung der Bakterien... 6 Zerstörung der Bakterien... 7 Trennung von Plasmid-DNA und genomischer DNA... 8 Reinigung der Plasmid-DNA... 10 Elution der gereinigten
Inhalt Einleitung... 2 Materialien... 4 Gewinnung der Bakterien... 6 Zerstörung der Bakterien... 7 Trennung von Plasmid-DNA und genomischer DNA... 8 Reinigung der Plasmid-DNA... 10 Elution der gereinigten
MutaREAL Cytomegalovirus real time PCR Kit
 MutaREAL Cytomegalovirus real time PCR Kit Screening Test für den Nachweis von humanen Cytomegaloviren (CMV) mittels real time PCR. KV2900324 KV2900396 Nur für Forschungszwecke Immundiagnostik AG, Stubenwald-Allee
MutaREAL Cytomegalovirus real time PCR Kit Screening Test für den Nachweis von humanen Cytomegaloviren (CMV) mittels real time PCR. KV2900324 KV2900396 Nur für Forschungszwecke Immundiagnostik AG, Stubenwald-Allee
3 GFP green fluorescent protein
 SCHNUPPERKURS GENTECHNIK 1 ExploHeidelberg 2 Klonierung des Phagen Lambda 3 GFP green fluorescent protein 4 Gens in a bottle Vanessa Hecht 1 ExploHeidelberg Stiftung Jugend und Wissenschaft GmbH Technologiepark
SCHNUPPERKURS GENTECHNIK 1 ExploHeidelberg 2 Klonierung des Phagen Lambda 3 GFP green fluorescent protein 4 Gens in a bottle Vanessa Hecht 1 ExploHeidelberg Stiftung Jugend und Wissenschaft GmbH Technologiepark
Versuchsanleitung: RFLP als Modell für einen DNA-Fingerprint
 RFLP als Modell für einen DNA-Fingerprint Teil 1: Restriktionsverdau 1.1: Thermoblock / Wasserbad auf 37 C vorheizen 1.2: Puffer Y+/Tango auftauen und auf Eis stellen 1.3: 4 Proben, RSA I und H 2 O demin.
RFLP als Modell für einen DNA-Fingerprint Teil 1: Restriktionsverdau 1.1: Thermoblock / Wasserbad auf 37 C vorheizen 1.2: Puffer Y+/Tango auftauen und auf Eis stellen 1.3: 4 Proben, RSA I und H 2 O demin.
Kapillarelektrophorese DNA-Sequenzierung
 Kapillarelektrophorese DNA-Sequenzierung DNA Kettenanalyse oder DNA-Sequenzierung wird bei der Anordnung der Primärstruktur und Bestimmung der Nukleotid-Basensequenz verwendet. Die Analyse basiert auf
Kapillarelektrophorese DNA-Sequenzierung DNA Kettenanalyse oder DNA-Sequenzierung wird bei der Anordnung der Primärstruktur und Bestimmung der Nukleotid-Basensequenz verwendet. Die Analyse basiert auf
Praktikum: Nachweis einer gentechnischen Veränderung in Lebensmitteln durch PCR
 Praktikum: Nachweis einer gentechnischen Veränderung in Lebensmitteln durch PCR Vorbereitung Lehrer Für jede Arbeitsgruppe werden 550 µl InstaGene-Matrix aliquotiert! Das Tube wird mit IG beschriftet!
Praktikum: Nachweis einer gentechnischen Veränderung in Lebensmitteln durch PCR Vorbereitung Lehrer Für jede Arbeitsgruppe werden 550 µl InstaGene-Matrix aliquotiert! Das Tube wird mit IG beschriftet!
Drosophila melanogaster
 Modul biol113 Zellbiologie Drosophila melanogaster Komponenten der angeborenen Immunabwehr Experimente 1) RT (Reverse Transkriptase)-PCR zum Nachweis einer AMP- Expression nach Infektion 1.1 PCR-Reaktion
Modul biol113 Zellbiologie Drosophila melanogaster Komponenten der angeborenen Immunabwehr Experimente 1) RT (Reverse Transkriptase)-PCR zum Nachweis einer AMP- Expression nach Infektion 1.1 PCR-Reaktion
Zeitaufgelöste Fluoreszenzmessung zur Verwendung bei der Realtime-PCR
 Zeitaufgelöste Fluoreszenzmessung zur Verwendung bei der Realtime-PCR Nils Scharke, inano Abstract Die Verwendung neuartiger Seltenerd-Komplexe in Verbindung mit zeitaufgelöster Fluoreszenzmessung liefert
Zeitaufgelöste Fluoreszenzmessung zur Verwendung bei der Realtime-PCR Nils Scharke, inano Abstract Die Verwendung neuartiger Seltenerd-Komplexe in Verbindung mit zeitaufgelöster Fluoreszenzmessung liefert
Das Reagenz speziell für die Transfektion von Säugerzellen mit sirna und mirna
 METAFECTENE SI + Das Reagenz speziell für die Transfektion von Säugerzellen mit sirna und mirna Bestellinformationen, MSDS, Publikationen und Anwendungsbeispiele unter www.biontex.com Produkt Katalognummer
METAFECTENE SI + Das Reagenz speziell für die Transfektion von Säugerzellen mit sirna und mirna Bestellinformationen, MSDS, Publikationen und Anwendungsbeispiele unter www.biontex.com Produkt Katalognummer
C V C. Gebrauchsanweisung für Biofortuna SSPGo TM HLA No Template Control Kit BF-40-02. Revision 2. Juli 2014
 DOT133v1 Instructions for Use Biofortuna SSPGo TM HLA No Template Control Kit BF-40-02 Seite 1 von 7 Gebrauchsanweisung für Biofortuna SSPGo TM HLA No Template Control Kit BF-40-02 Revision 2 Juli 2014
DOT133v1 Instructions for Use Biofortuna SSPGo TM HLA No Template Control Kit BF-40-02 Seite 1 von 7 Gebrauchsanweisung für Biofortuna SSPGo TM HLA No Template Control Kit BF-40-02 Revision 2 Juli 2014
Werte für Menschen, Tiere und Umwelt. Dermatophyten-PCR. synlab.vet Fachinformation
 Werte für Menschen, Tiere und Umwelt Dermatophyten-PCR synlab.vet Fachinformation Dermatophyten-PCR Ergebnisse einer vergleichenden Studie von kultureller mykologischer Untersuchung und PCR-Untersuchung.
Werte für Menschen, Tiere und Umwelt Dermatophyten-PCR synlab.vet Fachinformation Dermatophyten-PCR Ergebnisse einer vergleichenden Studie von kultureller mykologischer Untersuchung und PCR-Untersuchung.
AmpFlSTR NGM SElect PCR-Amplifizierungs-Kit PCR-Amplifizierung und Kapillarelektrophorese
 KURZANLEITUNG AmpFlSTR NGM SElect PCR-Amplifizierungs-Kit PCR-Amplifizierung und Kapillarelektrophorese Hinweis: Richtlinien zur Sicherheit und Biogefährdung finden Sie im Anhang Sicherheit im AmpFlSTR
KURZANLEITUNG AmpFlSTR NGM SElect PCR-Amplifizierungs-Kit PCR-Amplifizierung und Kapillarelektrophorese Hinweis: Richtlinien zur Sicherheit und Biogefährdung finden Sie im Anhang Sicherheit im AmpFlSTR
Informationsveranstaltung Heimtierfuttermittel. PCR-Analytik zur Bestimmung von GVOs in Heimtierfuttermitteln. C. Haldemann, ALP
 Informationsveranstaltung Heimtierfuttermittel PCR-Analytik zur Bestimmung von GVOs in Heimtierfuttermitteln C. Haldemann, ALP Grundidee des Nachweises von GVOs mittels PCR Die Bestimmung genveränderter
Informationsveranstaltung Heimtierfuttermittel PCR-Analytik zur Bestimmung von GVOs in Heimtierfuttermitteln C. Haldemann, ALP Grundidee des Nachweises von GVOs mittels PCR Die Bestimmung genveränderter
Auf der Suche nach der Wundermedizin
 Auf der Suche nach der Wundermedizin Experimente im Schullabor 1 Herausgeber Novartis Pharma AG, CH-4002 Basel Autoren: Dr. Gesche Standke und Dr. Christiane Röckl Michel Zeichnungen: Fonds der Chemischen
Auf der Suche nach der Wundermedizin Experimente im Schullabor 1 Herausgeber Novartis Pharma AG, CH-4002 Basel Autoren: Dr. Gesche Standke und Dr. Christiane Röckl Michel Zeichnungen: Fonds der Chemischen
Produktinformation Saturn-2D REDOX Labeling Kit
 Saturn-2D REDOX Labeling Kit Produktinformation Saturn-2D REDOX Labeling Kit Produkt-Nr. PR34, PR35 NH DyeAGNOSTICS GmbH Weinbergweg 23 D-06120 Halle Deutschland Technischer Support Fon: +49 (0) 345-2799
Saturn-2D REDOX Labeling Kit Produktinformation Saturn-2D REDOX Labeling Kit Produkt-Nr. PR34, PR35 NH DyeAGNOSTICS GmbH Weinbergweg 23 D-06120 Halle Deutschland Technischer Support Fon: +49 (0) 345-2799
Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers
 Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers FIGURE 20.1 Biology 6/e Biotechnologie Protein Expression Genomische DNA PCR Vektormolekül (Plasmid) Escherichia coli
Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers FIGURE 20.1 Biology 6/e Biotechnologie Protein Expression Genomische DNA PCR Vektormolekül (Plasmid) Escherichia coli
F-I Molekulare Zoologie: Teil I: Expressionsanalysen. Expressionsanalyse mittels RT-PCR
 F-I Molekulare Zoologie: Teil I: Expressionsanalysen Expressionsanalyse mittels RT-PCR Inhalt: Seite I. Generelles 1 II. RNA-Aufreinigung mit EZNA Total RNA Kit (PeqLab)...2 III. Umschreiben von RNA in
F-I Molekulare Zoologie: Teil I: Expressionsanalysen Expressionsanalyse mittels RT-PCR Inhalt: Seite I. Generelles 1 II. RNA-Aufreinigung mit EZNA Total RNA Kit (PeqLab)...2 III. Umschreiben von RNA in
Real-time RT-PCR Testkit zum Nachweis des Virus der Klassischen Schweinepest
 V3_2011-03-21 VIROTYPE CSFV Gebrauchsinformation Real-time RT-PCR Testkit zum Nachweis des Virus der Klassischen Schweinepest in vitro-diagnostikum für Schweine Die deutsche Gebrauchsinformation ist nach
V3_2011-03-21 VIROTYPE CSFV Gebrauchsinformation Real-time RT-PCR Testkit zum Nachweis des Virus der Klassischen Schweinepest in vitro-diagnostikum für Schweine Die deutsche Gebrauchsinformation ist nach
Entwicklung und Validierung der VIROTYPE BVDV real-time RT-PCR
 Entwicklung und Validierung der real-time RT-PCR Gaunitz C, Engemann C, Labitzke M, Schroeder C, Kühn TE, Gabert, J Labor Diagnostik GmbH Leipzig Gliederung Testprinzip Testprotokoll Testcharakteristik
Entwicklung und Validierung der real-time RT-PCR Gaunitz C, Engemann C, Labitzke M, Schroeder C, Kühn TE, Gabert, J Labor Diagnostik GmbH Leipzig Gliederung Testprinzip Testprotokoll Testcharakteristik
bactotype MAP PCR Kit Gebrauchsinformation
 April 2015 bactotype MAP PCR Kit Gebrauchsinformation 24 (Katalog-Nr. 285903) 96 (Katalog-Nr. 285905) 480 (Katalog-Nr. 285907)* 1 Zum Nachweis von DNA von Mycobacterium avium subsp. paratuberculosis Die
April 2015 bactotype MAP PCR Kit Gebrauchsinformation 24 (Katalog-Nr. 285903) 96 (Katalog-Nr. 285905) 480 (Katalog-Nr. 285907)* 1 Zum Nachweis von DNA von Mycobacterium avium subsp. paratuberculosis Die
GEBRAUCHSANLEITUNG. Glutatione Agarose Resin
 GEBRAUCHSANLEITUNG Glutatione Agarose Resin Agarose zur Affinitätsreinigung von GST-Tag-Fusionsproteinen und anderen Glutathion-Bindungsproteinen (Kat.-Nr. 42172) SERVA Electrophoresis GmbH - Carl-Benz-Str.
GEBRAUCHSANLEITUNG Glutatione Agarose Resin Agarose zur Affinitätsreinigung von GST-Tag-Fusionsproteinen und anderen Glutathion-Bindungsproteinen (Kat.-Nr. 42172) SERVA Electrophoresis GmbH - Carl-Benz-Str.
Auf der Suche nach der Wundermedizin
 Auf der Suche nach der Wundermedizin Experimente im Schullabor 1 Herausgeber Novartis Pharma AG, CH-4002 Basel Autoren: Dr. Gesche Standke und Dr. Christiane Röckl Michel Zeichnungen: Fonds der Chemischen
Auf der Suche nach der Wundermedizin Experimente im Schullabor 1 Herausgeber Novartis Pharma AG, CH-4002 Basel Autoren: Dr. Gesche Standke und Dr. Christiane Röckl Michel Zeichnungen: Fonds der Chemischen
DiversiLab TM Schnelle und reproduzierbare Stammtypisierung
 DIVERSILABTM DiversiLab TM Schnelle und reproduzierbare Stammtypisierung 2/24 Weshalb Stammtypisierung? Eine Stammtypisierung dient nicht zur Identifizierung eines Erregers sondern um abzuklären, ob zwei
DIVERSILABTM DiversiLab TM Schnelle und reproduzierbare Stammtypisierung 2/24 Weshalb Stammtypisierung? Eine Stammtypisierung dient nicht zur Identifizierung eines Erregers sondern um abzuklären, ob zwei
Applications Note 229 August 2010
 Applications Note 229 August 2010 Weiterverwendung von mehrfach in Eppendorf BioPhotometer plus TM und UVette gemessenen DNA- Proben für PCR- und real-time PCR Experimente Martin Armbrecht, Nils Gerke,
Applications Note 229 August 2010 Weiterverwendung von mehrfach in Eppendorf BioPhotometer plus TM und UVette gemessenen DNA- Proben für PCR- und real-time PCR Experimente Martin Armbrecht, Nils Gerke,
Produktinformation Instrumentendesinfektion BASIS Konzentrat ID 200. Aldehydfreier Instrumenten-Desinfektionsreiniger. Allgemeine Hinweise:
 Aldehydfreier Instrumenten-Desinfektionsreiniger nach neuesten Richtlinien und Gutachten geprüft Korrosionsschutz, sehr gute Materialverträglichkeit Eignung auch für Ultraschallbäder großes Wirkungsspektrum
Aldehydfreier Instrumenten-Desinfektionsreiniger nach neuesten Richtlinien und Gutachten geprüft Korrosionsschutz, sehr gute Materialverträglichkeit Eignung auch für Ultraschallbäder großes Wirkungsspektrum
ZytoFast DNA (+) Control Probe
 ZytoFast DNA (+) Control Probe (Digoxigenin-markiert) T-1053-400 40 (0,4 ml) Zum Nachweis humaner repetitiver Alu-Sequenzen durch chromogene in situ Hybridisierung (CISH).... In-Vitro-Diagnostikum gemäß
ZytoFast DNA (+) Control Probe (Digoxigenin-markiert) T-1053-400 40 (0,4 ml) Zum Nachweis humaner repetitiver Alu-Sequenzen durch chromogene in situ Hybridisierung (CISH).... In-Vitro-Diagnostikum gemäß
SingleQuant Assay Kit
 GEBRAUCHSANLEITUNG SingleQuant Assay Kit Kit für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39226) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010
GEBRAUCHSANLEITUNG SingleQuant Assay Kit Kit für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39226) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010
Der Missing Link. Eppendorf Tubes 5.0 ml einfach und sicher mit System
 Der Missing Link 5.0 ml einfach und sicher mit System 2 In Kombination mit dem umfangreichen Zubehör-Sortiment sind 5.0 ml die perfekte Alternative für die Arbeit mit mittleren Probenvolumina! 3 5.0 ml
Der Missing Link 5.0 ml einfach und sicher mit System 2 In Kombination mit dem umfangreichen Zubehör-Sortiment sind 5.0 ml die perfekte Alternative für die Arbeit mit mittleren Probenvolumina! 3 5.0 ml
Methodensammlung des LAG PCR-Nachweis der p35s / pat - Genkassette in transgenen Kulturpflanzen
 Methodensammlung des LAG PCR-Nachweis der p35s / pat - Genkassette in transgenen Kulturpflanzen erstellt vom Unterausschuß Methodenentwicklung des LAG Status: verabschiedet 1 Zweck und Anwendungsbereich
Methodensammlung des LAG PCR-Nachweis der p35s / pat - Genkassette in transgenen Kulturpflanzen erstellt vom Unterausschuß Methodenentwicklung des LAG Status: verabschiedet 1 Zweck und Anwendungsbereich
Bradford Reagent, 5x
 GEBRAUCHSANLEITUNG Bradford Reagent, 5x Reagenz für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39222) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 HeidelbergPhone +49-6221-138400, Fax +49-6221-1384010
GEBRAUCHSANLEITUNG Bradford Reagent, 5x Reagenz für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39222) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 HeidelbergPhone +49-6221-138400, Fax +49-6221-1384010
ZytoFast DNA (+) Control Probe
 ZytoFast DNA (+) Control Probe (Biotin-markiert) T-1022-100 10 (0,1 ml) Zum Nachweis humaner repetitiver Alu-Sequenzen durch chromogene in situ Hybridisierung (CISH) Nur für Forschungszwecke bestimmt Biotin-markierte
ZytoFast DNA (+) Control Probe (Biotin-markiert) T-1022-100 10 (0,1 ml) Zum Nachweis humaner repetitiver Alu-Sequenzen durch chromogene in situ Hybridisierung (CISH) Nur für Forschungszwecke bestimmt Biotin-markierte
Anwendungsbericht zur Herstellung des Proteins GST-GFP-NLS
 Anwendungsbericht zur Herstellung des Proteins GST-GFP-NLS Von: Andreas Tschammer, Fachhochschule Aalen-Hochschule f. Technik und Wirtschaft, Fachbereich Chemie, Schwerpunkt Molekulare Biotechnologie Material
Anwendungsbericht zur Herstellung des Proteins GST-GFP-NLS Von: Andreas Tschammer, Fachhochschule Aalen-Hochschule f. Technik und Wirtschaft, Fachbereich Chemie, Schwerpunkt Molekulare Biotechnologie Material
Hohe Sensitivität und Spezifität: Alle Komponenten sind genauestens aufeinander abgestimmt
 BACTOTYPE PCR Amplification Kit Mycoplasma synoviae Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE Amplification Kit umfasst optimierte Systeme zum Nachweis von pathogenen Bakterien mittels
BACTOTYPE PCR Amplification Kit Mycoplasma synoviae Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE Amplification Kit umfasst optimierte Systeme zum Nachweis von pathogenen Bakterien mittels
Squish PCR: Zeitsparende Methode zur Genotypisierung von Drosophila Stämmen
 Squish PCR: Zeitsparende Methode zur Genotypisierung von Drosophila Stämmen Einleitung: Drosophila melanogaster hat sich als Modellorganismus in der Entwicklungsbiologie und der Genetik bewährt, und findet
Squish PCR: Zeitsparende Methode zur Genotypisierung von Drosophila Stämmen Einleitung: Drosophila melanogaster hat sich als Modellorganismus in der Entwicklungsbiologie und der Genetik bewährt, und findet
Reagenzien Isolierung von Nukleinsäuren
 Aufbewahrung bei Raumtemperatur Anwendung Isolierung ultrareiner Plasmid-DNA aus Bakterienkulturen von 1 ml bis 800 ml. Die Plasmid-DNA eignet sich für Manuelle und automatisierte Sequenzierung mit Fluoreszenzfarbstoffen
Aufbewahrung bei Raumtemperatur Anwendung Isolierung ultrareiner Plasmid-DNA aus Bakterienkulturen von 1 ml bis 800 ml. Die Plasmid-DNA eignet sich für Manuelle und automatisierte Sequenzierung mit Fluoreszenzfarbstoffen
Gebrauchsanleitung ChromoQuant QF-PCR Kit P/N 412.001-48
 Gebrauchsanleitung ChromoQuant QF-PCR Kit P/N 412.001-48 ChromoQuant Das ChromoQuant in vitro Diagnose-Set QF-PCR 1 zur Analyse von häufigen chromosomalen Erkrankungen der Chromosomen 13, 18 und 21 412.001-48u
Gebrauchsanleitung ChromoQuant QF-PCR Kit P/N 412.001-48 ChromoQuant Das ChromoQuant in vitro Diagnose-Set QF-PCR 1 zur Analyse von häufigen chromosomalen Erkrankungen der Chromosomen 13, 18 und 21 412.001-48u
1. Proteinnachweis mit Bradford-Farbreagenz
 1. Proteinnachweis mit Bradford-Farbreagenz 96-well-Platte Pipetten (10, 20 und 200 µl) Pipettenspitzen Proteinvorratslösung (1 mg/ml Albumin in destillierten Wasser) Destilliertes Wasser Bradford Farbreagenz
1. Proteinnachweis mit Bradford-Farbreagenz 96-well-Platte Pipetten (10, 20 und 200 µl) Pipettenspitzen Proteinvorratslösung (1 mg/ml Albumin in destillierten Wasser) Destilliertes Wasser Bradford Farbreagenz
PCR-Nachweis der pssuara / bar - Genkassette in transgenen Kulturpflanzen
 Methodensammlung des LAG PCR-Nachweis der pssuara / bar - Genkassette in transgenen Kulturpflanzen erstellt vom Unterausschuß Methodenentwicklung des LAG Status: verabschiedet 1. Zweck und Anwendungsbereich
Methodensammlung des LAG PCR-Nachweis der pssuara / bar - Genkassette in transgenen Kulturpflanzen erstellt vom Unterausschuß Methodenentwicklung des LAG Status: verabschiedet 1. Zweck und Anwendungsbereich
Etablierung einer. Homemade - PCR
 Etablierung einer Homemade - PCR Anja Schöpflin Institut für Pathologie Universitätsklinikum Freiburg Überblick: Anwendungsgebiete der PCR Anforderungen an Primer Auswahl geeigneter Primer / Primerdesign
Etablierung einer Homemade - PCR Anja Schöpflin Institut für Pathologie Universitätsklinikum Freiburg Überblick: Anwendungsgebiete der PCR Anforderungen an Primer Auswahl geeigneter Primer / Primerdesign
Hohe Sensitivität und Spezifität: Alle Komponenten sind genauestens aufeinander abgestimmt
 BACTOTYPE PCR Amplification Kit Mycoplasma gallisepticum Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE PCR Amplification Kit umfasst optimierte Systeme zum Nachweis von pathogenen Bakterien
BACTOTYPE PCR Amplification Kit Mycoplasma gallisepticum Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE PCR Amplification Kit umfasst optimierte Systeme zum Nachweis von pathogenen Bakterien
Vaterschaftsanalyse über DNA-Profile
 Vaterschaftsanalyse über DNA-Profile I. Einleitung Diese Anleitung erläutert das genetische Verfahren der Vaterschaftsanalyse, so wie es heute zum Einsatz kommt. Im vorliegenden Experimentier-Kit sind
Vaterschaftsanalyse über DNA-Profile I. Einleitung Diese Anleitung erläutert das genetische Verfahren der Vaterschaftsanalyse, so wie es heute zum Einsatz kommt. Im vorliegenden Experimentier-Kit sind
Status: verabschiedet. Alternativ kann zur Kontrolle ein 248 bp-fragment aus dem Raps- spezifischen pepc-gen (Phosphoenolpyruvate-Carboxylase)
 Methodensammlung des LAG PCR-Nachweis der 35S-nptII-Übergangssequenz, der pnapin-bayte- Übergangssequenz und des plsc-gens erstellt vom Unterausschuss Methodenentwicklung des LAG Status: verabschiedet
Methodensammlung des LAG PCR-Nachweis der 35S-nptII-Übergangssequenz, der pnapin-bayte- Übergangssequenz und des plsc-gens erstellt vom Unterausschuss Methodenentwicklung des LAG Status: verabschiedet
PyroMark Q24 Cartridge
 PyroMark Q24 Cartridge Version 2 Für das Dispensieren von Nukleotiden und Reagenzien im PyroMark Q24 MDx Für in-vitro-diagnostische Anwendungen 979302 1062816DE QIAGEN GmbH, QIAGEN-Straße 1, D-40724 Hilden
PyroMark Q24 Cartridge Version 2 Für das Dispensieren von Nukleotiden und Reagenzien im PyroMark Q24 MDx Für in-vitro-diagnostische Anwendungen 979302 1062816DE QIAGEN GmbH, QIAGEN-Straße 1, D-40724 Hilden
Restriktion zweier Plasmide zur Erstellung einer physikalischen Karte, Grundlagen der DNA- Trennung und Analyse über Agarosegele
 Versuch 1: Restriktionsenzyme als molekulare Werkzeuge Versuchsinhalt Restriktion zweier Plasmide zur Erstellung einer physikalischen Karte, Grundlagen der DNA- Trennung und Analyse über Agarosegele Zwei
Versuch 1: Restriktionsenzyme als molekulare Werkzeuge Versuchsinhalt Restriktion zweier Plasmide zur Erstellung einer physikalischen Karte, Grundlagen der DNA- Trennung und Analyse über Agarosegele Zwei
HybriScan I Pediococcus damnosus
 HybriScan I Pediococcus damnosus Molekularbiologisches Schnelltestsystem zur Identifizierung von Pediococcus damnosus Produkt-Nr.: 67289 Kontaktinformationen: HybriScan - Schnelltestsystem (F&E) Dr. Helmut
HybriScan I Pediococcus damnosus Molekularbiologisches Schnelltestsystem zur Identifizierung von Pediococcus damnosus Produkt-Nr.: 67289 Kontaktinformationen: HybriScan - Schnelltestsystem (F&E) Dr. Helmut
Biotechnologie Forscher TM. Genes in a Bottle Kit DNA Necklace Module
 Biotechnologie Forscher TM Genes in a Bottle Kit DNA Necklace Module Bestellnummer 166 2200 EDU für 18 Schüler Bestellen Sie 2 Module für 36 Schüler Nur für den Schulgebrauch. 1 Gene in der Flasche Isolieren
Biotechnologie Forscher TM Genes in a Bottle Kit DNA Necklace Module Bestellnummer 166 2200 EDU für 18 Schüler Bestellen Sie 2 Module für 36 Schüler Nur für den Schulgebrauch. 1 Gene in der Flasche Isolieren
Hohe Sensitivität und Spezifität: Alle Komponenten sind genauestens aufeinander abgestimmt
 BACTOTYPE PCR Amplification Kit Pasteurella multocida Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE PCR Amplification Kit umfasst optimierte Systeme zum Nachweis von pathogenen Bakterien mittels
BACTOTYPE PCR Amplification Kit Pasteurella multocida Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE PCR Amplification Kit umfasst optimierte Systeme zum Nachweis von pathogenen Bakterien mittels
peqgold TriFast FL Methode für die gleichzeitige Extraktion von RNA, DNA und Proteinen aus flüssigen Proben.
 peqgold TriFast FL Methode für die gleichzeitige Extraktion von RNA, DNA und Proteinen aus flüssigen Proben. Best.-Nr. 30-2110 100 ml 30-2120 200 ml 30-2130 500 ml Lagerung: Lichtgeschützt bei 4 C für
peqgold TriFast FL Methode für die gleichzeitige Extraktion von RNA, DNA und Proteinen aus flüssigen Proben. Best.-Nr. 30-2110 100 ml 30-2120 200 ml 30-2130 500 ml Lagerung: Lichtgeschützt bei 4 C für
Hohe Sensitivität und Spezifität: Alle Komponenten sind genauestens aufeinander abgestimmt
 BACTOTYPE PCR Amplification Kit Chlamydia sp. Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE PCR Amplification Kit umfasst optimierte Systeme zum Nachweis von pathogenen Bakterien mittels Polymerasekettenreaktion
BACTOTYPE PCR Amplification Kit Chlamydia sp. Gebrauchsanweisung Technologie Die Produktgruppe BACTOTYPE PCR Amplification Kit umfasst optimierte Systeme zum Nachweis von pathogenen Bakterien mittels Polymerasekettenreaktion
Klassifizierung: noch nicht abgeschlossen, Verwandtschaftsverhältnis zur Familie: Desulvovibrionaceae - Vertreter Desulvovibrio desulfuricans
 AVID X / 1998 Lawsonia intracellularis Seite -1- Klassifizierung: noch nicht abgeschlossen, Verwandtschaftsverhältnis zur Familie: Desulvovibrionaceae - Vertreter Desulvovibrio desulfuricans 1. ALLGEMEINES
AVID X / 1998 Lawsonia intracellularis Seite -1- Klassifizierung: noch nicht abgeschlossen, Verwandtschaftsverhältnis zur Familie: Desulvovibrionaceae - Vertreter Desulvovibrio desulfuricans 1. ALLGEMEINES
Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR)
 PCR Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR) von Kary B. Mullis entwickelt (1985) eigentlich im Mai 1983 bei einer nächtlichen Autofahrt erstes erfolgreiches Experiment am 16.12.1983
PCR Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR) von Kary B. Mullis entwickelt (1985) eigentlich im Mai 1983 bei einer nächtlichen Autofahrt erstes erfolgreiches Experiment am 16.12.1983
Zur Registrierung der Proben sind folgende Angaben auf dem Auftragsschein wichtig:
 Probentransport Zur Registrierung der Proben sind folgende Angaben auf dem Auftragsschein wichtig: Datum der Probenentnahme Uhrzeit der Probenentnahme Vollständige Patientendaten (Name, Vorname, Geburtsdatum
Probentransport Zur Registrierung der Proben sind folgende Angaben auf dem Auftragsschein wichtig: Datum der Probenentnahme Uhrzeit der Probenentnahme Vollständige Patientendaten (Name, Vorname, Geburtsdatum
Praktikumsteil: 3 - RACE-PCR und Klonierung von MADS-Box- Genen aus Monokotylen
 Praktikumsteil: 3 - RACE-PCR und Klonierung von MADS-Box- Genen aus Monokotylen Vorbereitung auf diesen Praktikumsteil: Organisation - Für den Bioinformatik-Teil benötigen Sie pro Gruppe einen Laptop -
Praktikumsteil: 3 - RACE-PCR und Klonierung von MADS-Box- Genen aus Monokotylen Vorbereitung auf diesen Praktikumsteil: Organisation - Für den Bioinformatik-Teil benötigen Sie pro Gruppe einen Laptop -
ZytoFast HPV High-Risk (HR) Types Probe (Digoxigenin
 ZytoFast HPV High-Risk (HR) Types Probe (Digoxigenin Digoxigenin-markiert markiert) T-1140-400 40 (0,4 ml) Zum Nachweis von Human Papilloma Virus (HPV) Typ 16/18/31/33/35/39/45/51/52/56/58/59/66/68/82
ZytoFast HPV High-Risk (HR) Types Probe (Digoxigenin Digoxigenin-markiert markiert) T-1140-400 40 (0,4 ml) Zum Nachweis von Human Papilloma Virus (HPV) Typ 16/18/31/33/35/39/45/51/52/56/58/59/66/68/82
Zusammenfassender Bericht der Feldstudie ulti med Schweiß-/ Oberflächen-Drogenscreening-System
 Zusammenfassender Bericht der Feldstudie ulti med Schweiß-/ Oberflächen-Drogenscreening-System Parameter (AMP/OPI/THC) (MTD/MET/COC) (AMP/OPI/THC) (PCP/ MET/COC) Produktnummer: 008S804 Produktnummer: 008S805
Zusammenfassender Bericht der Feldstudie ulti med Schweiß-/ Oberflächen-Drogenscreening-System Parameter (AMP/OPI/THC) (MTD/MET/COC) (AMP/OPI/THC) (PCP/ MET/COC) Produktnummer: 008S804 Produktnummer: 008S805
ZytoDot CEN X Probe. Zum Nachweis der humanen alpha-satelliten von Chromosom X durch chromogene in situ Hybridisierung (CISH) In-Vitro-Diagnostikum
 ZytoDot CEN X Probe C-3025-400 40 (0,4 ml) Zum Nachweis der humanen alpha-satelliten von Chromosom X durch chromogene in situ Hybridisierung (CISH).... In-Vitro-Diagnostikum gemäß EU-Richtlinie 98/79/EG
ZytoDot CEN X Probe C-3025-400 40 (0,4 ml) Zum Nachweis der humanen alpha-satelliten von Chromosom X durch chromogene in situ Hybridisierung (CISH).... In-Vitro-Diagnostikum gemäß EU-Richtlinie 98/79/EG
In welchen Stoffen befinden sich Laugen, wozu werden sie verwendet?
 Naturwissenschaften - Chemie - Säuren, Basen, Salze - 2 Basen (P7158700) 2.2 Laugen - Bestandteil von Haushaltsreinigern Experiment von: Phywe Gedruckt: 15.10.2013 11:55:39 intertess (Version 13.06 B200,
Naturwissenschaften - Chemie - Säuren, Basen, Salze - 2 Basen (P7158700) 2.2 Laugen - Bestandteil von Haushaltsreinigern Experiment von: Phywe Gedruckt: 15.10.2013 11:55:39 intertess (Version 13.06 B200,
Facharbeit. Restriktionsverdau am Plasmid puc 18 mit verschiedenen Enzymen
 Bernhard Strigel Gymnasium Kollegstufe/ Jahrgang: 2007/ 2009 Memmingen Leistungskurs: Biologie Kollegiat: Stefanie Funk Facharbeit Restriktionsverdau am Plasmid puc 18 mit verschiedenen Enzymen Abgegeben
Bernhard Strigel Gymnasium Kollegstufe/ Jahrgang: 2007/ 2009 Memmingen Leistungskurs: Biologie Kollegiat: Stefanie Funk Facharbeit Restriktionsverdau am Plasmid puc 18 mit verschiedenen Enzymen Abgegeben
Die Liste der S-Sätze mit entsprechenden P-Sätzen erhebt keinen Anspruch auf Vollständigkeit.
 Übersetzungstabelle* zwischen Sicherheitsratschlägen (S-Sätze gemäß RL 67/548/EWG) und Sicherheitshinweisen (P-Sätze gemäß Verordnung (EG) Nr. 1272/2008) Die Liste der S-Sätze mit entsprechenden P-Sätzen
Übersetzungstabelle* zwischen Sicherheitsratschlägen (S-Sätze gemäß RL 67/548/EWG) und Sicherheitshinweisen (P-Sätze gemäß Verordnung (EG) Nr. 1272/2008) Die Liste der S-Sätze mit entsprechenden P-Sätzen
Bijsluiter DE versie Imaverol 100 mg (glas) B. PACKUNGSBEILAGE 1
 B. PACKUNGSBEILAGE 1 GEBRAUCHSINFORMATION Imaverol 100 mg, Konzentrat zur örtlichen Anwendung 1.NAME UND ANSCHRIFT DES ZULASSUNGSINHABERS UND, WENN UNTERSCHIEDLICH, DES HERSTELLERS, DER FÜR DIE CHARGENFREIGABE
B. PACKUNGSBEILAGE 1 GEBRAUCHSINFORMATION Imaverol 100 mg, Konzentrat zur örtlichen Anwendung 1.NAME UND ANSCHRIFT DES ZULASSUNGSINHABERS UND, WENN UNTERSCHIEDLICH, DES HERSTELLERS, DER FÜR DIE CHARGENFREIGABE
Plasmidisolierung. Mit Plasmiden können Sie Gene in Organismen einschleusen und so deren Eigenschaften verändern.
 Plasmidisolierung Mit Plasmiden können Sie Gene in Organismen einschleusen und so deren Eigenschaften verändern. Was können Sie lernen? Sie lernen eine ringförmige DNA, ein Plasmid, zu isolieren. Mit diesem
Plasmidisolierung Mit Plasmiden können Sie Gene in Organismen einschleusen und so deren Eigenschaften verändern. Was können Sie lernen? Sie lernen eine ringförmige DNA, ein Plasmid, zu isolieren. Mit diesem
Standardabweichung und Variationskoeffizient. Themen. Prinzip. Material TEAS Qualitätskontrolle, Standardabweichung, Variationskoeffizient.
 Standardabweichung und TEAS Themen Qualitätskontrolle, Standardabweichung,. Prinzip Die Standardabweichung gibt an, wie hoch die Streuung der Messwerte um den eigenen Mittelwert ist. Sie ist eine statistische
Standardabweichung und TEAS Themen Qualitätskontrolle, Standardabweichung,. Prinzip Die Standardabweichung gibt an, wie hoch die Streuung der Messwerte um den eigenen Mittelwert ist. Sie ist eine statistische
Versuch 6.14 ph-abhängigkeit eines Indikators am Beispiel Thymolblau
 Versuch 6.14 ph-abhängigkeit eines Indikators am Beispiel Thymolblau Einleitung Lösungen mit verschiedenen ph-werten von stark sauer bis stark basisch werden mit gleich viel Thymolblau-Lösung versetzt.
Versuch 6.14 ph-abhängigkeit eines Indikators am Beispiel Thymolblau Einleitung Lösungen mit verschiedenen ph-werten von stark sauer bis stark basisch werden mit gleich viel Thymolblau-Lösung versetzt.
GHS-Einstufung und Kennzeichnung der verwendeten Gefahrstoffe
 Lernen durch Lehren im Fachgebiet Chemie GHS-Einstufung und Kennzeichnung der verwendeten Gefahrstoffe (Quellen: http://gestis.itrust.de/nxt/gateway.dll/gestis_de/000000.xml?f=templates$fn=default.htm$3.0,
Lernen durch Lehren im Fachgebiet Chemie GHS-Einstufung und Kennzeichnung der verwendeten Gefahrstoffe (Quellen: http://gestis.itrust.de/nxt/gateway.dll/gestis_de/000000.xml?f=templates$fn=default.htm$3.0,
piccolo Analyzer Kurzbedienungsanleitung Leitfaden zur Probengewinnung Zur umfassenden Information benutzen Sie bitte das piccolo Bedienerhandbuch
 Kurzbedienungsanleitung Leitfaden zur Probengewinnung Zur umfassenden Information benutzen Sie bitte das piccolo Bedienerhandbuch Abaxis, Inc. 3240 Whipple Road Union City, CA 94587 TESTDURCHFUEHRUNG MIT
Kurzbedienungsanleitung Leitfaden zur Probengewinnung Zur umfassenden Information benutzen Sie bitte das piccolo Bedienerhandbuch Abaxis, Inc. 3240 Whipple Road Union City, CA 94587 TESTDURCHFUEHRUNG MIT
Isolierung von Nukleinsäuren (DNA) aus Formalin-fixierten Paraffingewebe-Schnitten (FFPE) DNA - Isolierung aus FFPE Schnitten Grundlagen
 Isolierung von Nukleinsäuren (DNA) aus Formalin-fixierten Paraffingewebe-Schnitten (FFPE) Grundlagen Fixierung DNA Isolierung Grundlagen Nukleotid: Zucker, Phosphor, Base Cytosin Guanin Thymin Adenin Bildquelle:
Isolierung von Nukleinsäuren (DNA) aus Formalin-fixierten Paraffingewebe-Schnitten (FFPE) Grundlagen Fixierung DNA Isolierung Grundlagen Nukleotid: Zucker, Phosphor, Base Cytosin Guanin Thymin Adenin Bildquelle:
HPV DNA-Chip. PapilloCheck HPV-Screening. DNA-Chip für die Identifizierung von 24 humanen Papillomavirus Typen
 HPV DNA-Chip PapilloCheck HPV-Screening DNA-Chip für die Identifizierung von 24 humanen Papillomavirus Typen PapilloCheck : schnell und zuverlässig PapilloCheck im Überblick Komplettes Kit mit DNA-Arrays
HPV DNA-Chip PapilloCheck HPV-Screening DNA-Chip für die Identifizierung von 24 humanen Papillomavirus Typen PapilloCheck : schnell und zuverlässig PapilloCheck im Überblick Komplettes Kit mit DNA-Arrays
Molekulare Verfahren im Kontext mit klinischer Praxis und Bestandsbetreuung beim Schwein
 Molekulare Verfahren im Kontext mit klinischer Praxis und Bestandsbetreuung beim Schwein DNA-Extraktion Photometrie Polymerase-Kettenreaktion (PCR) Restriktionsanalyse Agarose-Gelelektrophorese Polyacrylamid-Gelelektrophorese
Molekulare Verfahren im Kontext mit klinischer Praxis und Bestandsbetreuung beim Schwein DNA-Extraktion Photometrie Polymerase-Kettenreaktion (PCR) Restriktionsanalyse Agarose-Gelelektrophorese Polyacrylamid-Gelelektrophorese
SERVAGel N Native Gel Precast Vertical Gels for native Electrophoresis
 GEBRAUCHSANLEITUNG SERVAGel N Native Gel Precast Vertical Gels for native Electrophoresis (Kat.-Nr. 43250, 43251, 43252, 43253) SERVA Electrophoresis GmbH - Carl-Benz-Str. 7-69115 Heidelberg Phone +49-6221-138400,
GEBRAUCHSANLEITUNG SERVAGel N Native Gel Precast Vertical Gels for native Electrophoresis (Kat.-Nr. 43250, 43251, 43252, 43253) SERVA Electrophoresis GmbH - Carl-Benz-Str. 7-69115 Heidelberg Phone +49-6221-138400,
Tierartbestimmung mittels spezifischer Polymerasekettenreaktion
 Einleitung Der Tierart-Kit SK1-12 enthält die notwendigen Materialien, um verarbeitete Tierarten in gängigen Fleisch- und Milchprodukten, z.b. Wurst oder Käse zu bestimmen. Ein Lehrerheft und fünf Schülerhefte,
Einleitung Der Tierart-Kit SK1-12 enthält die notwendigen Materialien, um verarbeitete Tierarten in gängigen Fleisch- und Milchprodukten, z.b. Wurst oder Käse zu bestimmen. Ein Lehrerheft und fünf Schülerhefte,
Molekulargenetischer Nachweis und Genotypisierung von HPV
 Molekulargenetischer Nachweis und Genotypisierung von HPV Dr. Sabine Sussitz-Rack Institut für Labordiagnostik und Mikrobiologie Vorstand: Prim. Prof. DDr. Pranav Sinha Humanes Papillomavirus HPV HPV ist
Molekulargenetischer Nachweis und Genotypisierung von HPV Dr. Sabine Sussitz-Rack Institut für Labordiagnostik und Mikrobiologie Vorstand: Prim. Prof. DDr. Pranav Sinha Humanes Papillomavirus HPV HPV ist
Praktikum: Einleitung zu den technischen Geräten. Die automatische Pipette
 Die automatische Pipette Die Pipette ist wohl das wichtigste Werkzeug bei der Laborarbeit. Ständig müssen kleine bzw. kleinste Flüssigkeitsvolumina im ml- bzw. μl-bereich dosiert werden. Dabei sind die
Die automatische Pipette Die Pipette ist wohl das wichtigste Werkzeug bei der Laborarbeit. Ständig müssen kleine bzw. kleinste Flüssigkeitsvolumina im ml- bzw. μl-bereich dosiert werden. Dabei sind die
Verbesserung der Qualitätssicherung KOLT
 Verbesserung der Qualitätssicherung bei Blutspenderscreening PCR Testung KOLT 11.11.2009 M. Schmidt, M. K. Hourfar, W. Sireis, E. Seifried Übersicht 7 Risiken in der PCR Präanalytische Bedingungen Zentrifugation
Verbesserung der Qualitätssicherung bei Blutspenderscreening PCR Testung KOLT 11.11.2009 M. Schmidt, M. K. Hourfar, W. Sireis, E. Seifried Übersicht 7 Risiken in der PCR Präanalytische Bedingungen Zentrifugation
Safety Integrated. Einführung und Begriffe zur funktionalen Sicherheit von Maschinen und Anlagen. Nachschlagewerk Januar Answers for industry.
 Siemens AG 2013 Einführung und Begriffe zur funktionalen Sicherheit von Maschinen und Anlagen Nachschlagewerk Januar 2013 Safety Integrated Answers for industry. Einführung und Begriffe zur funktionalen
Siemens AG 2013 Einführung und Begriffe zur funktionalen Sicherheit von Maschinen und Anlagen Nachschlagewerk Januar 2013 Safety Integrated Answers for industry. Einführung und Begriffe zur funktionalen
Die Liste der S-Sätze mit entsprechenden P-Sätzen erhebt keinen Anspruch auf Vollständigkeit.
 Übersetzungstabelle* zwischen Sicherheitsratschlägen (S-Sätze gemäß RL 67/548/EWG) und Sicherheitshinweisen (P-Sätze gemäß Verordnung (EG) Nr. 1272/2008) Die Liste der S-Sätze mit entsprechenden P-Sätzen
Übersetzungstabelle* zwischen Sicherheitsratschlägen (S-Sätze gemäß RL 67/548/EWG) und Sicherheitshinweisen (P-Sätze gemäß Verordnung (EG) Nr. 1272/2008) Die Liste der S-Sätze mit entsprechenden P-Sätzen
Die Liste der S-Sätze mit entsprechenden P-Sätzen erhebt keinen Anspruch auf Vollständigkeit.
 Übersetzungstabelle* zwischen Sicherheitsratschlägen (S-Sätze gemäß RL 67/548/EWG) und Sicherheitshinweisen (P-Sätze gemäß Verordnung (EG) Nr. 1272/2008) Die Liste der S-Sätze mit entsprechenden P-Sätzen
Übersetzungstabelle* zwischen Sicherheitsratschlägen (S-Sätze gemäß RL 67/548/EWG) und Sicherheitshinweisen (P-Sätze gemäß Verordnung (EG) Nr. 1272/2008) Die Liste der S-Sätze mit entsprechenden P-Sätzen
cobas T HSV 1/2 Test Erweiterung Ihres STI Menüs mit Dual-Target Detektion für zuverlässige Befunde
 cobas T HSV 1/2 Test Erweiterung Ihres STI Menüs mit Dual-Target Detektion für zuverlässige Befunde Zuverlässige HSV 1/2 Ergebnisse, zukunftssicher Herpes simplex Viren zählen zu den am häufigsten sexuell
cobas T HSV 1/2 Test Erweiterung Ihres STI Menüs mit Dual-Target Detektion für zuverlässige Befunde Zuverlässige HSV 1/2 Ergebnisse, zukunftssicher Herpes simplex Viren zählen zu den am häufigsten sexuell
Qualitätskontrolle von Lebensmitteln: Was esse ich wirklich?
 Qualitätskontrolle von Lebensmitteln: Was esse ich wirklich? Im Unterricht habt ihr bereits einige Methoden und Vorgehensweisen der Molekularbiologie kennengelernt. Aber wo finden diese Methoden im täglichen
Qualitätskontrolle von Lebensmitteln: Was esse ich wirklich? Im Unterricht habt ihr bereits einige Methoden und Vorgehensweisen der Molekularbiologie kennengelernt. Aber wo finden diese Methoden im täglichen
Befall mit der Tropilaelapsmilbe
 Amtliche Methodensammlung Befall mit der Tropilaelapsmilbe (Tropilaelaps spp.) 1. Charakterisierung der Infektion 2. Untersuchungsmaterial 3. Untersuchungsgang Amtliche Methodensammlung des FLI Stand 15.05.2014
Amtliche Methodensammlung Befall mit der Tropilaelapsmilbe (Tropilaelaps spp.) 1. Charakterisierung der Infektion 2. Untersuchungsmaterial 3. Untersuchungsgang Amtliche Methodensammlung des FLI Stand 15.05.2014
Western Blot. Zuerst wird ein Proteingemisch mit Hilfe einer Gel-Elektrophorese aufgetrennt.
 Western Blot Der Western Blot ist eine analytische Methode zum Nachweis bestimmter Proteine in einer Probe. Der Nachweis erfolgt mit spezifischen Antikörpern, die das gesuchte Protein erkennen und daran
Western Blot Der Western Blot ist eine analytische Methode zum Nachweis bestimmter Proteine in einer Probe. Der Nachweis erfolgt mit spezifischen Antikörpern, die das gesuchte Protein erkennen und daran
Zuckernachweis mit Tollens-Reagenz
 Zuckernachweis mit Tollens-Reagenz Betriebsanweisung nach 0 Gefahrstoffverordnung Verwendete Chemikalien Bezeichnung R-Sätze S-Sätze Gefährlichkeitsmerkmale Silbernitrat (öllenstein) AgN 3 3-0/3 6--60-61
Zuckernachweis mit Tollens-Reagenz Betriebsanweisung nach 0 Gefahrstoffverordnung Verwendete Chemikalien Bezeichnung R-Sätze S-Sätze Gefährlichkeitsmerkmale Silbernitrat (öllenstein) AgN 3 3-0/3 6--60-61
