2 Material und Methoden
|
|
|
- Alma Richter
- vor 8 Jahren
- Abrufe
Transkript
1 2 Material und Methoden Alle Chemikalien wurden, wenn im Text nicht anders erwähnt, von den Firmen Sigma-Aldrich, München, Deutschland; Merck, Darmstadt, Deutschland; Fisher Scientific GmbH, Schwerte, Deutschland und Carl Roth GmbH, Karlsruhe, Deutschland bezogen. Es wurden stets Substanzen in höchster verfügbarer Reinheit verwendet. Chemikalien für molekularbiologische Methoden wurden in spezieller molekularbiologischer Qualität, d.h. RNase- und DNase-frei eingesetzt. Die Herstellung sämtlicher Lösungen erfolgte, wenn nicht anders angegeben, mit destilliertem als Lösungsmittel. Zur graphischen Darstellung der Ergebnisse und statistischen Analyse wurden, wenn nicht anders beschrieben, die Programme GraphPad Prism und GraphPad Instat (GraphPad Software, San Diego, CA, USA) genutzt. 2.1 Zellkultur Kultivierung der Zellen Die SN56.B5.G4-Zelllinie wurde durch Fusion der murinen Neuroblastom-Zelllinie N18TG2 mit Zellen aus dem Septum von 21-Tage alten Mäusen (Stamm: C57BL/6) erzeugt (Hammond et al., 1990). Die Zelllinie wurde von Prof. Dr. B. Wainer, Atlanta, Georgia, USA zur Verfügung gestellt. Die Kultivierung der SN56.B5.G4-Zellen erfolgte in Dulbecco`s modified Eagle`s medium (Biochrom AG, Berlin, Deutschland) mit 9 % fötalem Kälberserum (Gibco BRL, Rockville, MD, USA), 2 mm L-Glutamin und Penicillin/Streptomycin ( IE/ µg) bei 37 C in einer Atmosphäre von 5 % CO 2 im Zellkulturinkubator (Heraeus BB16, Osterode, Deutschland). Für die Kultivierung und zur RNA- und Proteingewinnung wurden T25-Zellkulturflaschen (Cellstar Greiner bio-one, Frickenhausen, Deutschland) verwendet. Für den MTT-Assay und Dichlorofluorescein-Assay wurden 96-Wellplatten; für die Immunhistochemie 24- Wellplatten (Cellstar Greiner bio-one, Frickenhausen, Deutschland) genutzt. Die Zellen wurden stets in einer Dichte von ~ 5000 Zellen/cm² ausgesät. Das Medium wurde aller zwei bis drei Tage gewechselt. Nach Erreichen einer Konfluenz von 90 % wurden die Zellen unter Verwendung von Trypsin (1x) (Gibco BRL, Rockville, MD, USA) gesplittet. 25
2 Die Differenzierung der Zellen wurde durch eine dreitägige Kultivierung mit 1 mm dibutyryl-camp und 1 µm Retinsäure erreicht (Jankowska et al., 1997; Szutowicz et al., 1999). Am zweiten Tag wurde das Medium erneuert. Nach erfolgter Differenzierung wurden die Zellen im entsprechenden Experiment verwendet und nicht mehr geteilt. Für die Versuche wurden nur Zellen bis zur Passage 40 genutzt Behandlung der Zellen Durch Zusatz von Aβ(1-42) (American Peptide, Sunnyvale, CA, USA) bzw. stoffperoxid zum Kulturmedium wurden die differenzierten Zellen mit den Noxen inkubiert. Vom stoffperoxid und Aβ(1-42) wurden zuvor Stocklösungen in HEPES 200 mm ph = 8,5 hergestellt. Kontrollzellen erhielten nur Zellkulturmedium mit einer entsprechenden Menge HEPES 200 mm ph = 8,5. Frisches Aβ(1-42) wurde unmittelbar nach Auflösung dem Zellkulturmedium zugefügt. Das Altern von Aβ(1-42) wurde durch eine sechstägige Präinkubation der Stocklösung bei 37 C erreicht. Die Inkubation mit den MAPK-Inhibitoren PD98059 (2-(2-Amino-3-methoxyphenyl)- 4H-1-benzopyran-4-on), SP (1,9-Pyrazoloanthron) und PD (4-(4- Fluorophenyl)-2-(4-nitrophenyl)-5-(4-pyridyl)-1H-imidazol) (Sigma-Aldrich, München, Deutschland) erfolgte entweder als Coinkubation gleichzeitig mit Aβ(1-42) oder in einer 24-stündigen Präinkubation des jeweiligen MAPK-Inhibitors; gefolgt von einer 24-stündigen Inkubation mit Aβ(1-42) nach Entfernung des MAPK-Inhibitors. Von PD98059, SP und PD wurden zuvor Stocklösungen in DMSO hergestellt Lichtmikroskopische Aufnahmen der Zellen Die Zellen wurden mit einem Nikon T300 Mikroskop mit integrierter Coolsnap Kamera (Nikon, Inc., El Segundo, CA, USA) unter Verwendung der Bildverarbeitungssoftware MetaMorph 5.0 (Universal Imaging Corporation, Downingtown, Pennsylvania, USA) sichtbar gemacht und dokumentiert. 26
3 2.2 Proteinbestimmung Die Proteinbestimmung erfolgte nach der Methode von Lowry (Lowry et al., 1951). Von der zu bestimmenden Proteinlösung wurden 20 µl in eine 96-Wellplatte vorgelegt. Nach Zugabe von 200 µl der Lösung C, die durch Mischen von Lösung A (2 % Na 2 CO 3 in 0,1 M NaOH) und Lösung B (0,5 % CuSO 4 in 1 % Natriumcitrat) im Verhältnis 1 : 50 frisch hergestellt wurde, und einer 10-minütigen Inkubation bei Raumtemperatur wurden zu jedem Well 20 µl 1 M Folinreagenzlösung zugefügt. Nach einer weiteren Inkubation von 20 min unter Lichtausschluss wurde die Absorption im Plattenphotometer (Anthos Labtec HT3, Salzburg, Österreich) bei 710 nm gemessen. Für die Eichkurve wurde Rinderserumalbumin (Serva, Heidelberg, Deutschland) in Konzentrationen zwischen 0,96-12 µg/20 µl verwendet. Es wurden Vierfachbestimmungen durchgeführt. 2.3 Radiochemische Bestimmung der Enzymaktivitäten Die Bestimmung der Enzymaktivitäten von Cholinacetyltransferase und Acetylcholinesterase in undifferenzierten und differenzierten SN56.B5.G4-Zellen erfolgte mit Hilfe von radiochemischen Assays. Die Zellen wurden in einer Dichte von 5000 Zellen/cm 2 in T25-Zellkulturflaschen ausgesät. Nach Anwachsen der Zellen auf dem Zellkulturflaschenboden wurde das Medium gewechselt. Die Hälfte der Flaschen erhielt weiter Kulturmedium, die andere Hälfte wurde für drei Tage in Differenzierungsmedium kultiviert. Anschließend erfolgte das Ernten durch Waschen und Abschaben der Zellen vom Flaschenboden mit Hilfe eines Zellschabers (Greiner bio-one, Frickenhausen, Deutschland) sowie die Aufnahme der abgelösten Zellen in 500 µl PBS- Puffer 0,1 M ph = 7,4. Von der Zellsuspensionen wurden 20 µl zur Proteinbestimmung verwendet, der verbleibende Teil wurde bis zur Enzymmessung bei - 20 C eingefrostet Aktivität der Cholinacetyltransferase Die Bestimmung der Aktivität der Cholinacetyltransferase basiert auf der radiochemischen Methode nach Fonnum, bei der tritiummarkiertes Acetyl-Coenzyme A und Cholinchlorid durch die Aktivität des Enzyms zu tritiummarkiertem Acetylcholin um- 27
4 gesetzt wird (Fonnum, 1975). Die aufgetauten Zellsuspensionen wurden mit Triton X- 100-haltiger 0,25 M Saccharose so verdünnt, dass sich eine Konzentration von ~ 1 µg/µl Protein und 0,2 % Triton X-100 in jeder Probe ergab. Durch Zugabe von 5 µl dieser Verdünnung zu einer vorbereiteten Substratmischung aus 0,28 mm [ 3 H]Acetylcoenzyme A (spezifische Aktivität: 7,4 TBq/mmol; PerkinElmer, Boston, MA, USA), 20 mm Cholinchlorid, 400 mm KCl, 0,4 mm EDTA, 0,2 mm Eserinsalicylat, 1 mg/ml Rinderserumalbumin und 40 mm Natriumphosphat-Puffer ph = 7,4 wurde die enzymatische Umsetzung gestartet. Von jeder Probe wurden Doppelbestimmungen eingesetzt. Nach 20-minütiger Inkubation bei 37 C erfolgte die Beendigung der Reaktion durch Waschen der Reaktionsgefäße mit 2,5 ml Natriumphosphat- Puffer 0,01 M ph = 7,4 und gleichzeitiger Überführung des gesamten Inhaltes in Szintillationsgefäße mit 1 ml Acetonitril und Natriumtetraphenylboron (5 mg/ml) sowie 5 ml Toluol-Szintillationscocktail. Die Szintillationsgefäße wurden kurz geschüttelt und zur Extraktion des gebildeten [ 3 H]Acetylcholins in die organische Phase ca. 20 min stehen gelassen. Anschließend wurde die Radioaktivität im Betacounter PW4700 (Philips, Hamburg, Deutschland) gemessen. Natriumphosphat-Puffer 0,01 M ph = 7,4: A) Na 2 HPO 4 1,78 g/1,0 l B) NaH 2 PO 4 1,38 g/1,0 l A) vorlegen, mit B) ph-wert auf 7,4 einstellen Toluol-Szintillationscocktail: 2,5-Diphenyloxazol 1,4-bis-[2-(5-Phenyloxazolyl)]benzen Isoamylalkohol Toluol 4,0 g 0,1 g 100 ml zu 1,0 l Aktivität der Acetylcholinesterase Zur Bestimmung der Aktivität der Acetylcholinesterase wurde der radiochemische Assay nach Johnson und Russell, 1975 verwendet. Die Zellsuspensionen wurden analog der Cholinacetyltransferase-Bestimmung verdünnt. Die Proteinkonzentration wurde auf ~ 0,5 µg/µl eingestellt. Es folgte die Zugabe von 10 µl dieser Verdünnung zu einer Lösung aus 50 µm [Acetyl- 3 H]-markierten Acetylcholin (spezifische Aktivität: 2,1 TBq/mmol; PerkinElmer, Boston, MA, USA) in Kaliumphosphat-Puffer 0,05 M ph 28
5 = 7,0. Nach einer Inkubation von 10 min bei Raumtemperatur wurde die enzymatische Acetylcholinesterase-Spaltung des radioaktiven Acetylcholins durch Zugabe von 100 µl einer Lösung aus 1 mm Chloressigsäure, 0,5 M NaOH und 2 M NaCl gestoppt. Nach Extraktion des gebildeten [ 3 H]Acetats in die organische Phase des Toluol-Szintillationscocktails wurden die radioaktiven Zerfälle im Betacounter (Philips, Hamburg, Deutschland) gemessen. Es wurden Dreifachbestimmungen durchgeführt. Kaliumphosphat-Puffer 0,05 M ph = 7,0: A) K 2 HPO 4 11,4 g/1,0 l B) KH 2 PO 4 6,8 g/1,0 l A) vorlegen, mit B) ph-wert auf 7,0 einstellen 2.4 Immunhistochemische Darstellung des vesikulären Acetylcholintransporters SN56.B5.G4-Zellen wurden auf Poly-(L)-Lysin-beschichtete Deckgläschen in 24- Wellplatten (Greiner bio-one, Frickenhausen, Deutschland) ausgesät und, wie unter 2.1.1, mit Kultur- oder Differenzierungsmedium behandelt. Nach drei Tagen wurde das Medium entfernt, die mit Zellen bewachsenen Deckgläschen mit PBS-Puffer 0,01 M ph = 7,4 gewaschen und anschließend für 10 min bei Raumtemperatur in 4 %-iger Paraformaldehyd-Lösung fixiert. Es folgte dreimaliges Waschen der Deckgläschen in TBS-Puffer 0,01 M ph = 7,4. Die unspezifischen Bindungsstellen wurden durch eine einstündige Behandlung mit 5 % Ziege-Normal-Serum (Dianova, Hamburg, Deutschland) in TBS-Puffer mit 0,3 % Triton X-100 bei Raumtemperatur unter leichtem Schütteln blockiert. Die Inkubation mit dem primären Antikörper Kaninchenpolyklonal-anti-VAChT 1 : 500 (Synaptic Systems, Göttingen, Deutschland) erfolgte in der gleichen Lösung bei Raumtemperatur über Nacht. Nach drei zehnminütigen Waschschritten in TBS-Puffer wurden die Zellen bei Raumtemperatur 1 h mit dem sekundären Antikörper Cy3-Ziege-anti-Kaninchen 20 µg/1 ml (Dianova, Hamburg, Deutschland) inkubiert. Nach zweimaligem Waschen für 5 min in TBS-Puffer 0,01 M ph = 7,4 und dreimaligem Waschen in destilliertem wurden die Deckgläschen an der Luft getrocknet und anschließend luftblasenfrei in einem Toluol/Entellan-Gemisch auf Objektträger aufgebracht. Die Aufnahme der immunhistochemischen Präparate erfolgte mit einem Zeiss Axiophot Mikroskop (Carl Zeiss, Je- 29
6 na, Deutschland) mit integrierter Kamera unter Verwendung der Software AxioVision (Carl Zeiss, Jena, Deutschland). TBS-Puffer 0,01 M ph = 7,4: Tris NaCl mit HCl auf ph = 7,4 einstellen 1,214 g 8,5 g zu 1,0 l 2.5 Fluorimetrischer Thioflavin T - Assay 20 µl des Aβ(1-42)-haltigen Zellkulturmediums wurden mit 50 mm Glycin ph = 9,5 und 2 µm Thioflavin T-Lösung zu einem Endvolumen von 200 µl verdünnt und in eine Fluoronunc 96-Wellplatte (Nunclon, Roskilde, Dänemark) unter Lichtschutz pipettiert. Anschließend erfolgte die Fluoreszenzmessung bei einer Absorptionswellenlänge von 435 nm und einer Emissionswellenlänge von 485 nm in einem Fluoreszenzspektrometer (Horiba Jobin Yvon, Edison, NJ, USA). Als Leerwert wurde die Fluoreszenz von Aβ(1-42)-freien Medium der Kontrollzellen verwendet. Alle Proben wurden als Dreifachbestimmung vermessen. 2.6 Native Polyacrylamid-Gelelektrophorese Vom Aβ(1-42)-haltigen Zellkulturmedium wurde ein ~ 10 µg Gesamtprotein entsprechendes Volumen im Verhältnis 1 : 5 mit Probenpuffer (5x) verdünnt und auf einem 10 %-igen nativen Polyacrylamid-Gel (Tab.1) unter Verwendung einer Standard- Elektrophoreseapparatur (BIO-RAD, Hercules, CA, USA) bei 120 V aufgetrennt. Zur Vermeidung von Proteindenaturierung durch entstehende Hitze wurde die Apparatur mit Eis gekühlt. Nach Auftrennung im Gel wurden die Proteine über Nacht bei 25 V auf eine PVDF-Membran (Immobilion transfer membranes, Millipore Corporation, Bedford, MA, USA; Porengröße: 0,2 µm) geblottet. Der Transfer wurde bei 4 C unter Verwendung einer Tankblot-Apparatur (BIO-RAD, Hercules, CA, USA) mit Blotpuffer (1x) durchgeführt. Zum Blocken wurde die Membran 45 min bei Raumtemperatur in 5 % Trockenmilch/TBST-Puffer unter leichtem Schütteln inkubiert. Anschließend erfolgte die Immunodetektion der Proteine. Dazu wurde die Membran 1 h bei Raumtemperatur unter Schütteln mit dem primären Antikörper Maus-anti-β-Amyloid, monoklonal 30
7 1 : 1000 (Chemicon International, Temecula, CA, USA) inkubiert. Nach dreimaligem Waschen für 3 min in TBST-Puffer schloss sich eine weitere Inkubation für 45 min bei Raumtemperatur mit dem sekundären Antikörper Ziege-anti-Maus IgG1-HRP 1 : 2000 (Santa Cruz, Santa Cruz, CA, USA) an. Beide Antikörper wurden in 5 % Trockenmilch/TBST-Puffer verdünnt. Die Membran wurde weitere siebenmal 5 min mit TBST-Puffer gewaschen. Zur Detektion der Banden wurde das ECL Western Blotting Detection System entsprechend den Herstellerangaben (Amersham Bioscience, Piscataway, NJ, USA) verwendet. Die Signale wurden mittels Autoradiographie unter Verwendung des Autoradiographie-Films Hyblot CL (Denville Scientific Inc., South Plainfield, NJ, USA) sichtbar gemacht. Sammelgel 3 %: Trenngel 10 %: 2,5 ml Tris-HCl 0,5 M ph = 6,8 - - Tris-HCl 1,5 M ph = 8,9 8,4 ml 1,0 ml Acrylamid 30 % 11,2 ml 6,4 ml 14,8 ml 100 µl APS 10 % 120 µl 10 µl TEMED 28 µl Tab.1. Zusammensetzung Sammel- und Trenngel der Nativen Polyacrylamid-Gelelektrophorese Probenpuffer (5x): Glycerol Tris-HCl 0,5 M ph = 6,8 Bromphenolblau 5 ml 2,7 ml 2,1 ml eine Spatelspitze Laufpuffer: Tris 0,05 M Glycin mit NaOH ph-wert auf 8,9 einstellen 18,2 g 79,8 g zu 3,0 l Blotpuffer (4x): Tris-Base Glycin 11,5 g 43,8 g zu 4,0 l 31
8 Blotpuffer (1x): Methanol Blotpuffer (4x) 500 ml 1,0 l 2,2 ml 2.7 MTT-Assay Der zur Vitalitätstestung verwendete MTT-Assay basiert auf der Umwandlung von 3- (4,5-Dimethylthiazol-2-yl)-2,5-diphenyltetrazoliumbromid (MTT) durch die Aktivität der mitochondrialen Dehydrogenasen lebender Zellen zum blau-violetten Formazan. SN56.B5.G4-Zellen wurden in 96-Wellplatte ausgesät, differenziert und mit Aβ(1-42), H 2 O 2 bzw. den MAPK-Inhibitoren behandelt (wie unter beschrieben). Nach entsprechender Inkubationszeit im Zellkulturbrutschrank wurde in jedes Well eine Mischung von MTT-Stammlösung (0,25 % in PBS-Puffer 0,01 M ph = 7,4) in Medium (10 µl/100 µl) pipettiert und für weitere 2 h mit den Zellen inkubiert. Die Lyse des in den vitalen Zellen gebildeten Farbstoffs erfolgte durch Zugabe von 100 µl Ethanol- DMSO (1:1) und 10-minütigem Schütteln bei Raumtemperatur. Die Absorption wurde bei 570 nm am Plattenphotometer (Dynex MRX, MTX Lab Systems, Inc., Vienna, VA, USA) gemessen. Es wurden mindestens Dreifachbestimmungen durchgeführt. PBS-Puffer 0,01 M ph = 7,4: A) Na 2 HPO 4 1,78 g/1,0 l B) NaH 2 PO 4 1,38 g/1,0 l A) vorlegen, mit B) ph-wert auf 7,4 einstellen NaCl 8,5 g/1,0 l 2.8 Dichlorofluorescein-Assay Zur Bestimmung intrazellulärer reaktiver Sauerstoffspezies (ROS) wurde 2`,7`- Dichlorodihydrofluoresceindiacetat (H 2 DCF-DA) als Sonde eingesetzt. H 2 DCF-DA penetriert die Zellmembran und wird in der Zelle durch ROS zum fluoreszierenden 2`,7`-Dichlorofluorescein umgewandelt. Die Umwandlung kann am Fluoreszenzspektrometer verfolgt werden. SN56.B5.G4-Zellen wurden in schwarze 96-Well-Fluoreszenzplatten mit Klarsichtboden (Greiner bio-one, Frickenhausen, Deutschland) gesät und, wie unter 2.1.1, beschrieben differenziert. Am Versuchstag wurde das Medium entfernt und die Zellen 32
9 vorsichtig mit PBS-Puffer 0,01 M ph = 7,4 (siehe 2.7) gewaschen. Es folgte eine 45- minütige Inkubation der Zellen mit 50 µm H 2 DCF-DA in phenolrotfreiem DMEM (Biochrom AG, Berlin, Deutschland) im Zellkulturbrutschank. Nach Entfernung des H 2 DCF-DA-haltigen Mediums und Waschen mit PBS-Puffer wurden die Zellen, wie unter 2.1.2, mit Aβ(1-42) oder H 2 O 2 behandelt und für entsprechende Zeit im Brutschank inkubiert. Medium/HEPES behandelte Zellen dienten als Kontrolle. Die Fluoreszenzmessung erfolgte zu Inkubationsbeginn sowie nach 1, 2, 4, 6, 12 und 24 h an einem HTS 7000 Bioassay Reader (PerkinElmer, Boston, MA, USA). Die Extinktionswellenlänge betrug 485 nm, die Emissionswellenlänge 520 nm. Es wurden Sechsfachbestimmungen durchgeführt. 2.9 DNA-Fragmentierung Die behandelten SN56.B5.G4-Zellen (siehe 2.1.2) wurden ohne vorherigen Mediumwechsel mit einer Pipette vom Boden der Zellkulturschale abgespült und durch anschließende Zentrifugation (MLW T62, Medizintechnik Leipzig, Leipzig, Deutschland) für 5 min bei 1000 rpm pelletiert. Der Überstand wurde verworfen, das Zellpellet in 1 ml PBS-Puffer 0,01 M ph = 7,4 resuspendiert und erneut für 2 min bei rpm (Eppendorf Centrifuge, 5417 R, Hamburg, Deutschland) zentrifugiert. Nach Suspendieren der Zellen in 500 µl Lysepuffer und Zugabe von 5 µl RNase A (10 mg/ml), erfolgte eine 40-minütige Inkubation bei 37 C auf dem Thermomixer (Eppendorf, Hamburg, Deutschland). Die in der Zellsuspension enthaltenen Proteine wurden durch Ausfällung mit 125 µl NaCl 5 M (60 min, 4 C) und anschließender Zentrifugation (15 min, rpm, 4 C) abgetrennt. Durch Chloroform-Phenol-Extraktion wurde die DNA aus dem Überstand extrahiert. Dazu wurden 250 µl Chloroform und 500 µl Rotiphenol (Carl-Roth GmbH, Karlsruhe, Deutschland) zum Überstand pipettiert und 2 min kräftig geschüttelt. Es folgte eine weitere Zentrifugation unter gleichen Bedingungen. Der Überstand des entstandenen Zweiphasengemisches wurde erneut mit 650 µl Chloroform versetzt, geschüttelt und zentrifugiert. Durch Zugabe von 1 ml eisgekühlten iso-propanol wurde die DNA über Nacht bei - 20 C ausgefällt. Die präzipitierte DNA wurde durch einen letzten Zentrifugationsschritt pelletiert, nach vorsichtigem Entfernen des Überstandes für ca. 10 min an der Luft getrocknet und schließlich in 30 µl TE-Puffer ph = 8,0 gelöst. 10 µl dieser Lösung wurden mit 5 µl DNA- Probenpuffer (1x) versetzt und für 5 min bei 65 C unter Schütteln inkubiert (Ther- 33
10 momixer, Eppendorf, Hamburg, Deutschland). Nach kurzem Abkühlen auf Eis erfolgte die Auftragung der Proben auf ein 1,75 %-iges DNA-Gel. Als Standard wurde ein 1 kbp und ein 100 bp DNA-Standard (Peqlab Biotechnologie GmbH, Erlangen, Deutschland) verwendet. Die Auftrennung der DNA wurde mit Hilfe einer Elektrophoreseapparatur (Easy Cast Elektrophoresis System; Biometra, Göttingen, Deutschland) bei 75 V durchgeführt. Zur Visualisierung der DNA-Banden wurde das Gel in einer Transilluminatoreinheit mit integrierter Kamera (Herolab GmbH, Wiesloch, Deutschland) betrachtet und anschließend fotografisch dokumentiert. Lysepuffer: Tris-HCl 1 M ph = 8,0 SDS 20 % EDTA 0,5 M 0,5 ml 1,5 ml 1,0 ml zu 50 ml TE-Puffer ph = 8,0: EDTA Tris 1 M ph = 8,0 DEPC- mit NaOH auf ph = 8,0 einstellen DEPC- 0,19 g 5 ml zu 400 ml zu 500 ml DNA-Gel: Agarose 1,75 g Ethidiumbromid (10 mg/ml) 4 µl TAE-Puffer (1x) zu 100 ml DNA-Probenpuffer (1x): Glycerol DEPC- Bromphenolblau 1 ml 1 ml eine Spatelspitze Laufpuffer: TAE-Puffer (1x) 34
11 TAE-Puffer (10x): Tris EDTA Eisessig auf ph = 8,5 einstellen 242 g 18,6 g 57 ml zu 1,0 l 2.10 Microarrays RNA-Extraktion Differenzierte SN56.B5.G4-Zellen wurden, wie unter beschrieben, mit 50 µm frischem Aβ(1-42), 250 µm H 2 O 2 oder HEPES (Kontrollzellen) behandelt. Nach einer 24-stündigen Inkubation wurde die Gesamt-RNA der Zellen unter Verwendung von Tri-Reagent (Molecular Research Center, Cincinnati, OH, USA) entsprechend den Vorschriften des Herstellers isoliert. Nach Chloroform-Extraktion und anschließender Fällung mit iso-propanol wurde das erhaltende RNA-Pellet in 20 µl Nuklease-freiem (Promega, Madison, WI, USA) gelöst. Die Qualität der RNA wurde durch Messung des OD 260/280 -Quotienten bestimmt. Dazu wurden 1 µl der RNA-Lösung in 100 µl TE-Puffer (siehe 2.9) verdünnt und an einem UV-Vis-Spektrometer Beckman DU-7400 (Beckman Coulter Inc. Fullerton, CA, USA) vermessen. Des Weiteren wurde die RNA auf einem RNA-Gel aufgetrennt. 2 µl der RNA-Lösung wurden mit 6 µl Probenpuffer für 15 min bei 65 C denaturiert und für ca. 2 h unter Verwendung einer Elektrophoreseapparatur (BIO-RAD, Hercules, CA, USA) bei 50 V aufgetrennt. Alle verwendeten Proben zeigten weder einen OD 260/280 -Quotient unter 1,7 noch eine sichtbare Degradierung auf dem RNA-Gel. RNA-Probenpuffer: Formamid 720 µl MOPS (10x) 160 µl Formaldehyd 260 µl Ethidiumbromid (10mg/ml) 1,5 µl Glycerol : (1:1) 160 µl DEPC- 190 µl Bromphenolblau eine Spatelspitze 35
12 RNA-Gel: Agarose DEPC- Formaldehyd (37 %) MOPS (10x) 1 g 73 ml 17 ml 10 ml MOPS (10x): MOPS Natriumacetat EDTA DEPC- 42 g 4,1 g 3,8 g zu 1,0 l RNA-Laufpuffer: MOPS (1x) Markierung und Hybridisierung der RNA Für die Genexpressionsanalyse wurden kommerziell erhältliche Affymetrix Gene- Chips Mouse Genome (Affymetrix, Santa Clara, CA, USA) verwendet. Ein Affymetrix GeneChip Mouse Genome enthält ~ Probesets, welche ~ Transcripts und Varianten von ~ murinen Genen kodieren. Von den Aβ(1-42)- und H 2 O 2 -behandelten Zellen sowie den Kontrollen wurden jeweils drei unabhängig behandelte RNA-Proben mit je drei Microarrays hybridisiert, so dass insgesamt neun Microarrays verwendet wurden. Alle Schritte wurden nach einem von der Firma Affymetrix empfohlenen Standardprotokoll durchgeführt. 20 ng der totalen RNA wurden unter Verwendung eines T7-Promotor enthaltenden Primers und Superscript II (Invitrogen Life Technologies, Carlsbad, CA, USA) in doppelsträngige cdna umgeschrieben. Die Extraktion der gebildeten cdna erfolgte mit Hilfe eines Phenol-Chloroform-Gemisches und anschließender Ethanol-Ammoniumacetat- Fällung. Die cdna diente als Template für die folgende in vitro Transkriptionsreaktion mit Biotin-markierten Nucleotiden (Enzo Life Science, Farmingdale, NY, USA; Affymetrix, Santa Clara, CA, USA). Die resultierende, biotinylierte crna wurde auf einer RNeasy-Säule (Qiagen, Valencia, CA, USA) gesammelt und anschließend für die Hybridisierung fragmentiert. Die Hybridisierung der crna mit den Arrays erfolgte an einer Affymetrix GeneChip Fluidics Workstation 400 (Affymetrix, Santa Clara, CA, USA). Nach Bindung mit Phycoerythrin-gekoppelten Avidin wurden die Chips mit einem Hewlett Packard GeneAr- 36
13 ray Scanner (Hewlett Packard Company, Palo Alto, CA, USA) gescannt. Die Image- Analyse erfolgte mit Unterstützung der Affymetrix GeneChip Analysis Software Microarray Suite 4.0 (Affymetrix, Santa Clara, CA, USA) Auswertung der Microarrays Die Analyse der Microarrays wurde im Wesentlichen in drei Schritten durchgeführt: 1. Normalisierung der Rohdaten, 2. statistische Analyse und Filterung, 3. Ontologische Einordnung der signifikant veränderten Gene und Literaturrecherche. Die nach Imageanalyse erhaltenen Affymetrix GeneChip probe array Files (CELund CHP-Files) der hybridisierten Microarrays wurden zunächst in das Softwareprogramm ArrayAssist (Stratagene, La Jolla, CA, USA) importiert, wo sie unter Verwendung des RMA-Algorithmus (Irizarry et al., 2003a) normalisiert wurden. Der RMA-Algorithmus stellt eine robuste Methode zur Normalisierung von Multi-Chip- Analysen dar. Alle Rohdaten wurden in die zentrale Datenbank des Europäischen Institutes für Bioinformatik ( geladen. Die normalisierten Expressionswerte jedes einzelnen Probesets wurden einer statistischen Auswertung unter Verwendung des Programms R ( unterzogen. Dazu wurden je drei Chips zu einer Gruppe zusammengefasst: 1. unbehandelte Kontrollzellen, µm Aβ(1-42)-behandelte Zellen sowie µm H 2 O 2 - behandelte Zellen. Unterschiede in der Genexpression zwischen den einzelnen Gruppen wurden für jedes Probeset mittels ANOVA-Statistik und anschließendem post-hoc Tukey-Test überprüft. Alle normalisierten Expressionswerte sowie die dazugehörigen, berechneten statistischen Parameter wurden in Microsoft EXCEL (Microsoft Corporation, Redmond, WA, USA) importiert, wo der gesamte Datensatz durch gezieltes Einsetzen von Filtern reduziert wurde. Für die manuelle Genontologie-Analyse wurden nur Probesets betrachtet, die eine Signifikanz von p 0,001 bei ANOVA und post-hoc Tukey-Test sowie eine Auf- bzw. Abregulation im Vergleich zur Kontrolle von 1,5 aufwiesen. Die Genontologie-Datenbank Amigo ( der Analyse Center von Affymetrix NetAffx TM ( und die Literaturdatenbank Pubmed ( dienten dabei als Hilfe. Zusätzlich wurde von allen signifikant veränderten Genen (p 0,001) eine Genontologie-Analyse unter Verwendung des Programms OntoExpress ( 37
14 express/) durchgeführt. OntoExpress berücksichtigt bei der ontologischen Eingliederung das biologische Gesamtprofil des Microarray und vergleicht dies mit dem Profil des signifikanten Datensatzes Quantitative real-time RT-PCR RNA-Extraktion Die RNA-Extraktion für die quantitative real-time RT-PCR wurde, wie unter beschrieben, durchgeführt Reverse Transkription und quantitative Amplifikation Zur Validierung der Ergebnisse der Microarrays wurden die Genexpressionsveränderungen einiger ausgewählter Gene zusätzlich mittels real-time RT-PCR bestimmt. Von jedem Gen wurden auch hier je drei unabhängige Proben pro Gruppe (1. Lösungsmittel-behandelte Kontrollzellen, µm Aβ(1-42)-behandelte Zellen sowie µm H 2 O 2 -behandelte Zellen) untersucht. Die RNA für die real-time RT-PCR wurde mit Hilfe eines Nanodrop Spektrophotometers (Nanodrop Technologies, Wilmington, DE, USA) quantifiziert. Die Qualität der RNA wurde durch Analyse auf einem RNA-Nanochip unter Verwendung des Agilent 2100 Bioanalyzer (Agilent Technologies, Palo Alto, CA, USA) geprüft. Zur Synthese der doppelsträngigen cdna wurden die Reagenzien des TaqMan Reverse Transcription Reagents Kits von Applied Biosystems (ABI #N , Applied Biosystems, Forster City, CA, USA) verwendet. Die Reaktionsbedingungen für die reverse Transkription waren folgende: 25 ºC, 10 min/48 ºC, 30 min/95 ºC, 5 min. Anschließend wurde die quantitative singleplex real-time Amplifikation durchgeführt. Dazu wurden 2 µl der synthetisierten cdna mit TaqMan MGB probes (FAM TM -markiert für das Targetgen; VIC TM -markiert für das Referenzgen) und dem TaqMan Universal PCR Master Mix (ABI # ) nach den Angaben des Herstellers (Applied Biosystems, Forster City, CA, USA) in einem Gesamtvolumen von 50 µl gemischt. Die Endkonzentration der cdna betrug 250 nm, die der Primer 900 nm. Die TaqMan MGB probes sowie die Primer wurden über die Accessions-Nummern (Acc.Nr.) der ausgewählten Gene ermittelt. Die Primer sind vom Hersteller vorgegeben und für diese 38
15 Reaktionsbedingungen optimiert. Die real-time PCR wurde an einem ABI Prism 7000 Sequence Detection System (Applied Biosystems, Forster City, CA, USA) unter folgenden Reaktionsbedingungen durchgeführt: 50 ºC, 2 min/95 ºC, 10 min/95 ºC, 15 s - 60 ºC, 1 min (40 Zyklen). Von jeder Probe wurde Dreifachbestimmungen ermittelt. Als Referenzgen zur Normalisierung diente 18S RNA Auswertung der real-time RT-PCR Die erhaltenen C T -Werte wurden anschließend in Microsoft EXCEL (Microsoft Corporation, Redmond, WA, USA) unter Verwendung der komparativen C T ( CT )- Methode von Applied Biosystems (Applied Biosystems, Forster City, CA, USA) ausgewertet. Dabei wurde die Menge des Targetgens (2 - CT ) durch Normalisierung zum Referenzgen und relativ zu einem Kalibrator (eine der Proben) berechnet. Die x- fache Genexpressionsveränderung wurde aus dem Quotienten der Menge des Targetgens in der jeweiligen Behandlungsgruppe und der Menge des Targetgens in der Kontrolle ermittelt. Die statistische Auswertung der real-time RT-PCR erfolgte, wie unter beschrieben, durch ANOVA Analyse und anschließendem post-hoc Tukey-Test im Softwareprogramm R ( Die Pearson-Korrelation wurde in Microsoft EXCEL (Microsoft Corporation, Redmond, WA, USA) berechnet Bestimmung von Proteinexpressionsveränderungen Proteinpräparation Differenzierte SN56.B5.G4-Zellen wurden, wie unter 2.1.2, mit 50 µm frischem Aβ(1-42) behandelt. Zu Inkubationsbeginn (0 h) sowie nach einer Behandlungsdauer von 2 h, 6 h, 12 h und 24 h wurde das Kulturmedium entfernt, die Zellen mit PBS-Puffer 0,01 M ph = 7,4 gewaschen, mit einem Zellkulturschaber vom Boden der T25- Kulturflasche gelöst und in 75 µl PBS-Puffer 0,01 M ph = 7,4 mit 15 % Protease- Inhibitorstocklösung (Complete EDTA free, Roche, Mannheim, Deutschland) und 1 % Phosphatase-Inhibitorcocktail II (Sigma-Aldrich, München, Deutschland) aufgenommen. Die Lyse der Zellen erfolgte durch Ultraschallbehandlung (3 x 5 s) unter Eiskühlung. Die Separierung des Zellhomogenates in Membranfraktion und cytosoli- 39
16 sche Fraktion wurde durch eine 15-minütige Zentrifugation (Eppendorf Centrifuge, 5417 R, Hamburg, Deutschland) bei x g und 4 C erreicht. Das erhaltene Pellet stellte die Membranfraktion dar, der Überstand bildete die cytosolische Fraktion. Das Membranpellet wurde in 25 µl des gleichen Protease-Phosphatase-Inhibitor- Mix in Lösung gebracht. Von allen Proben wurden 5 µl zur Proteinbestimmung entnommen, der restliche Teil wurde bis zur Verwendung für SDS-PAGE/Western Blotting bei - 20 C aufbewahrt SDS-Polyacrylamid-Gelelektrophorese und Western-Blotting Für die Proteinanalytik wurde eine denaturierende SDS-Polyacrylamid- Gelelektrophorese (SDS-PAGE) nach Laemmli (Laemmli et al., 1970) durchgeführt. Die Methode ermöglicht eine Auftrennung der Proteine entsprechend ihres Molekulargewichtes. Die nach aufbereiteten Zellhomogenate wurden aufgetaut, mit Solubilizer im Verhältnis 1 : 3 verdünnt, im Thermomixer Compact (Eppendorf, Hamburg, Deutschland) für 3 min bei 85 C denaturiert und bis zur Auftragung auf ein Polyacrylamid-Gel auf Eis gelagert. Für die semiquantitative Proteinanalytik war es erforderlich gleiche Proteinmengen jeder Probe auf einem Gel einzusetzen. In Abhängigkeit von der Sensitivität der verwendeten Antikörper und der Zellhomogenatfraktion wurden Proteinmengen zwischen 25 µg und 70 µg aufgetragen. Sammelgel 4 %: Trenngel 10 %: 2,5 ml Tris-HCl 0,5 M ph = 6,8 - - Tris-HCl 1,5 M ph = 8,9 2,5 ml 1,3 ml Acrylamid 30 % 3,3 ml 6,1 ml 4,1 ml 50 µl SDS 10 % 100 µl 75 µl APS 10 % 75 µl 15 µl TEMED 7,5 µl Tab.2. Zusammensetzung Sammel- und Trenngel der SDS-Polyacrylamid-Gelelektrophorese Die Auftrennung der Proteine erfolgte in einem 1,5 mm dicken Polyacrylamid-Gel bestehend aus einem 4 %-igen Sammel- und einem 10 %-igen Trenngel (Tab.2) in einer Standard-Elektrophoreseapparatur Mini-Protean II Cell mit Elektrophorese Modell 2000/2.0 Power Supply (BIO-RAD, Hercules, CA, USA) und Laufpuffer. Die 40
17 Elektrophoresegeschwindigkeit betrug 10 V/cm im Sammel- und 20 V/cm im Trenngel. Als Molekulargewichtsstandard wurde Prestained SDS-PAGE Standard Low Range (BIO-RAD, Hercules, CA, USA) eingesetzt. Nach der SDS-PAGE folgte ein 90-minütiger Transfer der elektrophoretisch aufgetrennten Proteine aus dem Polyacrylamid-Gel auf eine PVDF-Membran (Roti -PVDF; Porengröße: 0,45 µm; Carl Roth, Karlsruhe, Deutschland) bei 50 V. Es wurde eine Tankblot-Apparatur Trans-Blot TM Cell mit Elektrophorese Modell 2000/2.0 Power Supply (BIO-RAD, Hercules, CA, USA) und Blotpuffer verwendet. Die PVDF- Membran wurde zuvor durch eine Präinkubation in Methanol für die Proteinbindung aktiviert. Solubilizer: Tris 0,5 M ph = 6,8 Glycerol 87 % SDS-Lösung 10 % Mercaptoethanol Bromphenolblau 1,0 ml 0,8 ml 1,6 ml 0,4 ml eine Spatelspitze Laufpuffer: Tris Glycin SDS 3,0 g 14,4 g 1,0 g zu 1,0 l Blotpuffer: Tris Glycin Methanol 9,08 g 43,24 g 600 ml zu 3,0 l Immunodetektion der Proteine Nach dem Western-Blotting wurden unspezifische Bindungsstellen der Membran durch eine einstündige Inkubation bei Raumtemperatur in 4 % Trockenmilch/TBST blockiert. Es folgte ein dreimaliges Waschen der Membran für 5 min in TBST. Daran schloss sich die Immunodetektion der Proteine an. Folgende Antikörper mit entsprechenden Konzentrationen und Inkubationszeiten wurden verwendet: 41
18 Protein Antikörper Spezies Hersteller Konzentration Inkubationszeit Fraktion Primäre Antikörper ERK p44/42 MAPK Antibody Kaninchen Cell Signaling 1 : 1000 über Nacht, cytosolisch IgG, polyklonal Denvers, MA, 4 C USA JNK SAPK/JNK (56G8) IgG, Kaninchen Cell Signaling 1 : 1000 über Nacht, cytosolisch monoklonal Denvers, MA, 4 C USA p38 p38 Kinase MAPK Antibody, Kaninchen Cell Signaling 1 : 1000 über Nacht, cytosolisch Denvers, MA, 4 C polyklonal USA c-jun c-jun (60A8) IgG Kaninchen Cell Signaling 1 : 1000 über Nacht, cytosolisch monoklonal Denvers, MA, 4 C USA p-erk phospho-p44/42 Kaninchen Cell Signaling 1 : 1000 über Nacht, cytosolisch (Thr202/Tyr204) (20G11), Denvers, MA, 4 C monoklonal USA p-jnk phospho-sapk/jnk Kaninchen Cell Signaling 1 : 1000 über Nacht, cytosolisch (Thr183/Tyr185) (98F2), Denvers, MA, 4 C monoklonal USA p-p38 phospho-p38 MAPK Kaninchen Cell Signaling 1 : 1000 über Nacht, cytosolisch (Thr180/Tyr182) (12F8), Denvers, MA, 4 C monoklonal USA p-c-jun p-c-jun (Ser73) IgG Kaninchen Cell Signaling 1 : 1000 über Nacht, cytosolisch polyklonal Denvers, MA, 4 C USA β-actin anti-β-actin Clone AC-15, Maus Sigma-Aldrich, 1 : h, cytosolisch monoklonal München, Deutschland RT Sekundäre Antikörper ERK, JNK, Anti-rabbit IgG, HRPlinked Cell Signaling 1 : h, p38, c-jun, Antibody Denvers, MA, RT p-erk, p- USA JNK, p-p38, p-c-jun β-actin POD-conjugated AffiniPure Dianova, Ham- 1 : h, anti-mouse IgG burg, Deutsch- land RT Tab.3. Übersicht über die verwendeten primären und sekundären Antikörper Die primären und sekundären Antikörper wurden in 4 % Rinderserumalbumin (Serva, Heidelberg, Deutschland) in TBST verdünnt. Zwischen der Inkubation mit dem primären und sekundären Antikörper wurde die Membran unter leichtem Schütteln 3 x 5 min mit TBST gewaschen. Nach Inkubation mit dem sekundären Antikörper erfolgte ein abschließendes Waschen der Membran in TBS 0,01 M ph = 7,4 (siehe 2.4). Die Detektion der Proteine erfolgte durch Chemilumineszenz. Dazu wurde die Membran 42
19 in einer Mischung aus 4 ml Lösung A, 1,2 µl H 2 O 2 (30 %) und 400 µl Lösung B ~ 1 min inkubiert und unverzüglich durch die Kamera einer Kodak Image Station 2000R mit Kodak Molecular Image Software, Version (Kodak, Stuttgart, Deutschland) aufgenommen. Je nach Signalstärke wurden Belichtungszeiten zwischen 1-4 min gewählt. Für die anschließende Detektion des Housekeeping-Proteins β-actin auf der gleichen Membran war ein Entfernen der gebundenen primären und sekundären Antikörper der ersten Immunodetektion durch Strippen erforderlich. Dazu wurde die Membran 1 h unter leichtem Schütteln bei Raumtemperatur in Stripping-Puffer inkubiert und anschließend 3 x 5 min in TBST gewaschen. Die Membran konnte nun erneut geblockt und die Proteinbanden von β-actin, wie oben beschrieben, durch Immunodetektion sichtbar gemacht werden. TBST: TBS-Puffer 0,01 M ph = 7,4 mit 0,1 % Tween 20 Stripping-Puffer: Glycin ph-wert auf 2-2,5 einstellen SDS Tween 20 1,5 g zu 100 ml 100 mg 1,0 g Lösung A: Tris ph-wert auf 8,6 einstellen Luminol 2,42 g zu 200 ml 50 mg Lösung B: p-hydroxycoumarinsäure DMSO 11 mg 10 ml Auswertung der Proteinexpressionsveränderungen Die semiquantitative Auswertung der Proteinexpressionsveränderungen erfolgte über eine densitometrische Messung mit Hilfe des Programms TINA Version 2.09g (Raytest, Straubenhardt, Deutschland). Von der optischen Dichte jeder Proteinbande wurde zunächst ein auf der gleichen Laufbahn bestimmter Hintergrundwert abgezo- 43
20 gen. Zur Normalisierung der Blots wurde auf jedem Blot die hintergrund-korrigierte optische Dichte der Bande des zu untersuchenden Proteins zum Mittelwert der hintergrund-korrigierten optischen Dichten von β-actin auf einem Blot ins Verhältnis gesetzt. Die optische Dichte der Bande des Zielproteins wurde prozentual auf β-actin bezogen berechnet. Die mittlere optische Dichte von β-actin wurde dabei als 100 % definiert. Die ermittelten prozentualen optischen Dichten des Proteins zum jeweiligen Untersuchungszeitpunkt wurden als Expressionswert betrachtet. Von jedem Protein und jedem Untersuchungszeitpunkt wurden mindestens drei unabhängige Blots mit unabhängig behandelten und aufbereiteten Zellhomogenaten analysiert. Die Expressionswerte der unabhängigen Untersuchungen wurden schließlich gemittelt und einer statistischen Auswertung in Microsoft EXCEL (Microsoft Corporation, Redmond, WA, USA) unterzogen. Es wurde die Proteinexpression jedes Untersuchungszeitpunktes mit der Expression zu Inkubationsbeginn (Zeitpunkt 0 h) verglichen. 44
Anwendungsbericht zur Herstellung des Proteins GST-GFP-NLS
 Anwendungsbericht zur Herstellung des Proteins GST-GFP-NLS Von: Andreas Tschammer, Fachhochschule Aalen-Hochschule f. Technik und Wirtschaft, Fachbereich Chemie, Schwerpunkt Molekulare Biotechnologie Material
Anwendungsbericht zur Herstellung des Proteins GST-GFP-NLS Von: Andreas Tschammer, Fachhochschule Aalen-Hochschule f. Technik und Wirtschaft, Fachbereich Chemie, Schwerpunkt Molekulare Biotechnologie Material
Protokoll Praktikum für Humanbiologie Studenten
 Protokoll Praktikum für Humanbiologie Studenten Teil A: Charakterisierung der Auswirkungen von γ Interferon auf die Protein und mrna Mengen in humanen A549 Lungenepithelzellen. Studentenaufgaben Tag 1
Protokoll Praktikum für Humanbiologie Studenten Teil A: Charakterisierung der Auswirkungen von γ Interferon auf die Protein und mrna Mengen in humanen A549 Lungenepithelzellen. Studentenaufgaben Tag 1
Western Blot. Zuerst wird ein Proteingemisch mit Hilfe einer Gel-Elektrophorese aufgetrennt.
 Western Blot Der Western Blot ist eine analytische Methode zum Nachweis bestimmter Proteine in einer Probe. Der Nachweis erfolgt mit spezifischen Antikörpern, die das gesuchte Protein erkennen und daran
Western Blot Der Western Blot ist eine analytische Methode zum Nachweis bestimmter Proteine in einer Probe. Der Nachweis erfolgt mit spezifischen Antikörpern, die das gesuchte Protein erkennen und daran
Praktikum Biochemie Einführung in die Molekularbiologie. Bettina Siebers
 Praktikum Biochemie Einführung in die Molekularbiologie Bettina Siebers Rekombinante Expression einer Esterase aus Pseudomonas aeruginosa in E. coli Polyacrylamide Gelelektrophorese (PAGE) Denaturierende
Praktikum Biochemie Einführung in die Molekularbiologie Bettina Siebers Rekombinante Expression einer Esterase aus Pseudomonas aeruginosa in E. coli Polyacrylamide Gelelektrophorese (PAGE) Denaturierende
SDS Polyacrylamidgelelektrophorese (SDS-PAGE) Mini-Gelträger nach Anleitung zusammenbauen. Saubere Handschuhe tragen!!!
 aktualisiert, 08.03.2011, Wera Roth1 SDS Polyacrylamidgelelektrophorese (SDS-PAGE) Anleitung für Minigele Mini-Gelträger nach Anleitung zusammenbauen. Saubere Handschuhe tragen!!! Glasscheiben ordentlich
aktualisiert, 08.03.2011, Wera Roth1 SDS Polyacrylamidgelelektrophorese (SDS-PAGE) Anleitung für Minigele Mini-Gelträger nach Anleitung zusammenbauen. Saubere Handschuhe tragen!!! Glasscheiben ordentlich
GEBRAUCHSANLEITUNG. Glutatione Agarose Resin
 GEBRAUCHSANLEITUNG Glutatione Agarose Resin Agarose zur Affinitätsreinigung von GST-Tag-Fusionsproteinen und anderen Glutathion-Bindungsproteinen (Kat.-Nr. 42172) SERVA Electrophoresis GmbH - Carl-Benz-Str.
GEBRAUCHSANLEITUNG Glutatione Agarose Resin Agarose zur Affinitätsreinigung von GST-Tag-Fusionsproteinen und anderen Glutathion-Bindungsproteinen (Kat.-Nr. 42172) SERVA Electrophoresis GmbH - Carl-Benz-Str.
Johannes Gutenberg-Universität Mainz Fachbereich Biologie, Institut für Zoologie Leitung: Prof. Dr. Wolfrum Datum: 15. April 2005
 Johannes Gutenberg-Universität Mainz Fachbereich Biologie, Institut für Zoologie Leitung: Prof. Dr. Wolfrum Datum: 15. April 2005 F1 Molekulare Zoologie Teil II: Expressionsanalyse Proteinexpressionsanalyse
Johannes Gutenberg-Universität Mainz Fachbereich Biologie, Institut für Zoologie Leitung: Prof. Dr. Wolfrum Datum: 15. April 2005 F1 Molekulare Zoologie Teil II: Expressionsanalyse Proteinexpressionsanalyse
SERVA Streptavidin Agarose Resin Agarosematrix zur Affinitätsreinigung von biotinylierten Biomolekülen
 GEBRAUCHSANLEITUNG SERVA Streptavidin Agarose Resin Agarosematrix zur Affinitätsreinigung von biotinylierten Biomolekülen (Kat.-Nr. 42177) SERVA Electrophoresis GmbH - Carl-Benz-Str. 7-69115 Heidelberg
GEBRAUCHSANLEITUNG SERVA Streptavidin Agarose Resin Agarosematrix zur Affinitätsreinigung von biotinylierten Biomolekülen (Kat.-Nr. 42177) SERVA Electrophoresis GmbH - Carl-Benz-Str. 7-69115 Heidelberg
Plasmidisolierung. Mit Plasmiden können Sie Gene in Organismen einschleusen und so deren Eigenschaften verändern.
 Plasmidisolierung Mit Plasmiden können Sie Gene in Organismen einschleusen und so deren Eigenschaften verändern. Was können Sie lernen? Sie lernen eine ringförmige DNA, ein Plasmid, zu isolieren. Mit diesem
Plasmidisolierung Mit Plasmiden können Sie Gene in Organismen einschleusen und so deren Eigenschaften verändern. Was können Sie lernen? Sie lernen eine ringförmige DNA, ein Plasmid, zu isolieren. Mit diesem
aktualisiert, 10.03.2011, Wera Roth, DE1 WESTERN BLOT
 1 aktualisiert, 10.03.2011, Wera Roth, DE1 WESTERN BLOT 1. Hinweise zu Membranen a. Nitrocellulose b. PVDF (alternativ) 2. Aufbau des Transfers a. Naßblot b. Semi-dry (alternativ) 3. Färben und Dokumentation
1 aktualisiert, 10.03.2011, Wera Roth, DE1 WESTERN BLOT 1. Hinweise zu Membranen a. Nitrocellulose b. PVDF (alternativ) 2. Aufbau des Transfers a. Naßblot b. Semi-dry (alternativ) 3. Färben und Dokumentation
2 Materialien. Materialien 15. 2.1 Histondeacetylaseinhibitoren (HDIs) Sigma-Aldrich, Deutschland. 2.2 Zelllinien und Zellkultur.
 Materialien 15 2 Materialien 2.1 Histondeacetylaseinhibitoren (HDIs) Substanz Butyrat Trichostatin A (TSA) Valproat Hersteller Sigma-Aldrich, Sigma-Aldrich, Sigma-Aldrich, 2.2 Zelllinien und Zellkultur
Materialien 15 2 Materialien 2.1 Histondeacetylaseinhibitoren (HDIs) Substanz Butyrat Trichostatin A (TSA) Valproat Hersteller Sigma-Aldrich, Sigma-Aldrich, Sigma-Aldrich, 2.2 Zelllinien und Zellkultur
Immunofluoreszenz-Markierung an kultivierten adhärenten Säugerzellen. Formaldehyd-Fixierung
 Immunofluoreszenz-Markierung an kultivierten adhärenten Säugerzellen Formaldehyd-Fixierung 2 Materialien Pinzetten Für das Handling der Zellen ist es empfehlenswert Pinzetten mit sehr feiner Spitze zu
Immunofluoreszenz-Markierung an kultivierten adhärenten Säugerzellen Formaldehyd-Fixierung 2 Materialien Pinzetten Für das Handling der Zellen ist es empfehlenswert Pinzetten mit sehr feiner Spitze zu
Bradford Reagent, 5x
 GEBRAUCHSANLEITUNG Bradford Reagent, 5x Reagenz für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39222) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 HeidelbergPhone +49-6221-138400, Fax +49-6221-1384010
GEBRAUCHSANLEITUNG Bradford Reagent, 5x Reagenz für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39222) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 HeidelbergPhone +49-6221-138400, Fax +49-6221-1384010
Funktionelle Organisation des Zellkerns: DNA-Methylierung in Drosophila
 Funktionelle Organisation des Zellkerns: DNA-Methylierung in Drosophila 01.-04.03.04 Joachim Marhold, Regine Garcia Boy, Natascha Kunert, Cora Mund, Frank Lyko Programm 01.03.04: Präparation genomischer
Funktionelle Organisation des Zellkerns: DNA-Methylierung in Drosophila 01.-04.03.04 Joachim Marhold, Regine Garcia Boy, Natascha Kunert, Cora Mund, Frank Lyko Programm 01.03.04: Präparation genomischer
Probe und Probenmenge Wassermenge Auftragspuffermenge 5 µl Kaninchenmuskelextrakt 50 µl 100 µl
 Arbeitsgruppe D 6 Clara Dees Susanne Duncker Anja Hartmann Kristin Hofmann Kurs 3: Proteinanalysen Im heutigen Kurs extrahierten wir zum einen Proteine aus verschiedenen Geweben eines Kaninchens und führten
Arbeitsgruppe D 6 Clara Dees Susanne Duncker Anja Hartmann Kristin Hofmann Kurs 3: Proteinanalysen Im heutigen Kurs extrahierten wir zum einen Proteine aus verschiedenen Geweben eines Kaninchens und führten
Protokoll zur Übung Ölanalyse
 Protokoll zur Übung Ölanalyse im Rahmen des Praktikums Betreuender Assistent Univ.Ass. Dipl.-Ing. Martin Schwentenwein Verfasser des Protokolls: Daniel Bomze 0726183 1 Theoretischer Hintergrund 1.1 Aufgabenstellung
Protokoll zur Übung Ölanalyse im Rahmen des Praktikums Betreuender Assistent Univ.Ass. Dipl.-Ing. Martin Schwentenwein Verfasser des Protokolls: Daniel Bomze 0726183 1 Theoretischer Hintergrund 1.1 Aufgabenstellung
Immunserologie III. ELISA, Western-blot, Dot-blot
 Immunserologie III. ELISA, Western-blot, Dot-blot Universität ität Pécs, Medizinische Fakul ultät Institut für Immunologie und Biotechnologie ie ELISA 1. - Grundlagen o Enzyme o Linked o Immuno o Sorbent
Immunserologie III. ELISA, Western-blot, Dot-blot Universität ität Pécs, Medizinische Fakul ultät Institut für Immunologie und Biotechnologie ie ELISA 1. - Grundlagen o Enzyme o Linked o Immuno o Sorbent
Western Blots. Johannes A. Schmid
 Western Blots Monoklonaler Anti-c-myc von Boehringer (#1667149)...2 Polyklonaler Anti-c-myc Tag 409-420(cat#06-549/Lot#14966)...2 Anti-X-Press (#46-0528/Lot#800969)...2 Monoklonaler Anti-P-Tag (H902-ascites)...3
Western Blots Monoklonaler Anti-c-myc von Boehringer (#1667149)...2 Polyklonaler Anti-c-myc Tag 409-420(cat#06-549/Lot#14966)...2 Anti-X-Press (#46-0528/Lot#800969)...2 Monoklonaler Anti-P-Tag (H902-ascites)...3
4.1. Herstellung, Aufreinigung und Nachweis eines CD33-spezifischen IgM-Antikörpers
 ERGEBNISSE 30 4. Ergebnisse 4.1. Herstellung, Aufreinigung und Nachweis eines CD33-spezifischen IgM-Antikörpers 4.1.1. Herstellung und Aufreinigung des Antikörpers CD33-spezifische IgM-Antikörper wurden
ERGEBNISSE 30 4. Ergebnisse 4.1. Herstellung, Aufreinigung und Nachweis eines CD33-spezifischen IgM-Antikörpers 4.1.1. Herstellung und Aufreinigung des Antikörpers CD33-spezifische IgM-Antikörper wurden
www.gbo.com/bioscience Gewebekultur 1 Zell- und Microplatten 2 HTS- 3 Immunologie/ HLA 4 Mikrobiologie/ Bakteriologie Mehrzweckgefäße 5 Röhrchen/
 13 Reaktions/ 2 HTS 1 Zell und 4 Mikrobiologie / 1 Zell und 2 HTS n 4 I 2 n Sondermodelle 4 I 3 Keimzählschale 4 I 3 Macroplatte 4 I 3 Kontaktschalen 4 I 4 Quadratische 4 I 4 CELLSTAR OneWell Plate TM
13 Reaktions/ 2 HTS 1 Zell und 4 Mikrobiologie / 1 Zell und 2 HTS n 4 I 2 n Sondermodelle 4 I 3 Keimzählschale 4 I 3 Macroplatte 4 I 3 Kontaktschalen 4 I 4 Quadratische 4 I 4 CELLSTAR OneWell Plate TM
Trennungsverfahren Techniken (in der Biologie)
 Trennungsverfahren Techniken (in der Biologie)? Biomoleküle können getrennt werden aufgrund ihrer - chemischen Eigenschaften: Ladung, Löslichkeit, Wechselwirkung mit spezifischen Reagenzen, Molmasse -
Trennungsverfahren Techniken (in der Biologie)? Biomoleküle können getrennt werden aufgrund ihrer - chemischen Eigenschaften: Ladung, Löslichkeit, Wechselwirkung mit spezifischen Reagenzen, Molmasse -
Abbildungsverzeichnis
 I INHALTSVERZEICHNIS Abkürzungen VI Abbildungsverzeichnis VIII I. Einleitung 1. Neurone und Axonwachstum 1 2. Oligodendrozyten und Myelin 3 3. Das Proteolipid Protein (PLP) 6 4. Mutationen im PLP-Gen und
I INHALTSVERZEICHNIS Abkürzungen VI Abbildungsverzeichnis VIII I. Einleitung 1. Neurone und Axonwachstum 1 2. Oligodendrozyten und Myelin 3 3. Das Proteolipid Protein (PLP) 6 4. Mutationen im PLP-Gen und
Linking Transcription to the Metabolic State
 Towards Systems Biology of the Chloroplast under Stress: Linking Transcription to the Metabolic State Dissertation Zur Erlangung des Akademischen Grades Doktor der Naturwissenschaften (Dr. rer. nat.) Fakultat
Towards Systems Biology of the Chloroplast under Stress: Linking Transcription to the Metabolic State Dissertation Zur Erlangung des Akademischen Grades Doktor der Naturwissenschaften (Dr. rer. nat.) Fakultat
LD BioScreen. Low Density Biochip Schnelltest-Systeme. Offenes System für Kompetitive Immunoassays. LD BioScreen
 LD BioScreen Low Density Biochip Schnelltest-Systeme Offenes System für Kompetitive Immunoassays LD BioScreen Die Alternative zur Mikrotiterplatte Für Assays im Forschungslabor Sie sparen Material, Zeit
LD BioScreen Low Density Biochip Schnelltest-Systeme Offenes System für Kompetitive Immunoassays LD BioScreen Die Alternative zur Mikrotiterplatte Für Assays im Forschungslabor Sie sparen Material, Zeit
Plasmidpräparation aus Bakterien Inhalt
 Inhalt Einleitung... 2 Materialien... 4 Gewinnung der Bakterien... 6 Zerstörung der Bakterien... 7 Trennung von Plasmid-DNA und genomischer DNA... 8 Reinigung der Plasmid-DNA... 10 Elution der gereinigten
Inhalt Einleitung... 2 Materialien... 4 Gewinnung der Bakterien... 6 Zerstörung der Bakterien... 7 Trennung von Plasmid-DNA und genomischer DNA... 8 Reinigung der Plasmid-DNA... 10 Elution der gereinigten
SERVALight EosUltra Western Blot Chemilumineszenz HRP Substrat Kit
 GEBRAUCHSANLEITUNG SERVALight EosUltra Western Blot Chemilumineszenz HRP Substrat Kit (Kat.-Nr. 42586) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010
GEBRAUCHSANLEITUNG SERVALight EosUltra Western Blot Chemilumineszenz HRP Substrat Kit (Kat.-Nr. 42586) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010
Transcriptomics: Analysis of Microarrays
 Transcriptomics: Analysis of Microarrays Dion Whitehead dion@uni-muenster.de Division of Bioinformatics, Westfälische Wilhelms Universität Münster Microarrays Vorlesungsüberblick : 1. Überblick von Microarray
Transcriptomics: Analysis of Microarrays Dion Whitehead dion@uni-muenster.de Division of Bioinformatics, Westfälische Wilhelms Universität Münster Microarrays Vorlesungsüberblick : 1. Überblick von Microarray
Titrationskurve einer starken Säure (HCl) mit einer starken Base (NaOH)
 Titrationskurve einer starken Säure (HCl) mit einer starken Base (NaOH) Material 250 mlbecherglas 100 ml Messzylinder 50 mlbürette, Magnetrührer, Magnetfisch, Stativmaterial phmeter Chemikalien Natronlauge
Titrationskurve einer starken Säure (HCl) mit einer starken Base (NaOH) Material 250 mlbecherglas 100 ml Messzylinder 50 mlbürette, Magnetrührer, Magnetfisch, Stativmaterial phmeter Chemikalien Natronlauge
merken!!! 29,22 g NaCl abwiegen, in einem Becher mit etwa 800 ml Wasser lösen, dann im Messzylinder auf 1000 ml auffüllen.
 Das ABC der Stöchiometrie Lösungen aus Feststoffen Molare Lösungen herstellen (m = M c V) Beispiel 1: 1 L einer 500 mm NaCl-Lösung herstellen. Masse: Volumen: Stoffmenge: Dichte: m (kg) V (L) n (mol) (kg/l)
Das ABC der Stöchiometrie Lösungen aus Feststoffen Molare Lösungen herstellen (m = M c V) Beispiel 1: 1 L einer 500 mm NaCl-Lösung herstellen. Masse: Volumen: Stoffmenge: Dichte: m (kg) V (L) n (mol) (kg/l)
Durchführung einer Gel-Elektrophorese mit einem DNA-Gemisch
 Durchführung einer Gel-Elektrophorese mit einem DNA-Gemisch (Fotos vom 6. März 2013 Molekularbiologisches Praktikum 12 G-Kurs Biologie Herr Korne - am KOMM Homburg/Saar unter Anleitung von Frau Dr. Amoroso)
Durchführung einer Gel-Elektrophorese mit einem DNA-Gemisch (Fotos vom 6. März 2013 Molekularbiologisches Praktikum 12 G-Kurs Biologie Herr Korne - am KOMM Homburg/Saar unter Anleitung von Frau Dr. Amoroso)
Praktikum: Nachweis einer gentechnischen Veränderung in Lebensmitteln durch PCR
 Praktikum: Nachweis einer gentechnischen Veränderung in Lebensmitteln durch PCR Vorbereitung Lehrer Für jede Arbeitsgruppe werden 550 µl InstaGene-Matrix aliquotiert! Das Tube wird mit IG beschriftet!
Praktikum: Nachweis einer gentechnischen Veränderung in Lebensmitteln durch PCR Vorbereitung Lehrer Für jede Arbeitsgruppe werden 550 µl InstaGene-Matrix aliquotiert! Das Tube wird mit IG beschriftet!
DNA Isolierung. Praktikum Dr. László Kredics
 Isolierung Praktikum Dr. László Kredics Aufgabe: Isolierung von Plasmid aus Bakterienzellen Plasmid : pbluescript Vektor, Gröβe: 2960 Bps 1. 1,5 ml Bakterienkultur in Eppendorf-Röhrchen pipettieren, 2
Isolierung Praktikum Dr. László Kredics Aufgabe: Isolierung von Plasmid aus Bakterienzellen Plasmid : pbluescript Vektor, Gröβe: 2960 Bps 1. 1,5 ml Bakterienkultur in Eppendorf-Röhrchen pipettieren, 2
Verzeichnis der Abkürzungen... 6. 1. Einleitung... 9
 Inhaltsverzeichnis Verzeichnis der Abkürzungen... 6 1. Einleitung... 9 1.1 Probiotika...9 1.1.1 Definition und Historisches...9 1.1.2 Klinische Bedeutung probiotisch wirksamer Bakterienstämme...9 1.1.3
Inhaltsverzeichnis Verzeichnis der Abkürzungen... 6 1. Einleitung... 9 1.1 Probiotika...9 1.1.1 Definition und Historisches...9 1.1.2 Klinische Bedeutung probiotisch wirksamer Bakterienstämme...9 1.1.3
Modul 4 SS 2015. Western Blot. Tag 1: Proteinbestimmung, SDS-PAGE-Gel-Herstellung S. 3. Tag 2: Gelelektrophorese, Western Blot, Blockierung S.
 Modul 4 SS 2015 Western Blot Tag 1: Proteinbestimmung, SDS-PAGE-Gel-Herstellung S. 3 Tag 2: Gelelektrophorese, Western Blot, Blockierung S. 6 Tag 3: Detektion der Proteine auf der Membran S. 10 1 Über
Modul 4 SS 2015 Western Blot Tag 1: Proteinbestimmung, SDS-PAGE-Gel-Herstellung S. 3 Tag 2: Gelelektrophorese, Western Blot, Blockierung S. 6 Tag 3: Detektion der Proteine auf der Membran S. 10 1 Über
8.1. Zusammensetzung und Herstellung der verwendeten Medien für die In-vitro-Maturation, -Fertilisation und - Kultivierung
 8. Anhang 8.1. Zusammensetzung und Herstellung der verwendeten Medien für die In-vitro-Maturation, -Fertilisation und - Kultivierung 1.) Spüllösung (modifizierte PBS-Lösung) modifizierte PBS-Lösung 500
8. Anhang 8.1. Zusammensetzung und Herstellung der verwendeten Medien für die In-vitro-Maturation, -Fertilisation und - Kultivierung 1.) Spüllösung (modifizierte PBS-Lösung) modifizierte PBS-Lösung 500
3,58 g 0,136 g. ad 100 ml
 9 Anhang 9.1 Rezepturen der Puffer und Lösungen 9.1.1 Vorbereitung der Proben zur Extraktion Coon s-puffer (0,1 M, ph 7,2-7,6) Na 2 HPO 4 x 12 H 2 O KH 2 PO 4 Aqua dest. 3,58 g 0,136 g 8,77 g 9.1.2 Aufbereitung
9 Anhang 9.1 Rezepturen der Puffer und Lösungen 9.1.1 Vorbereitung der Proben zur Extraktion Coon s-puffer (0,1 M, ph 7,2-7,6) Na 2 HPO 4 x 12 H 2 O KH 2 PO 4 Aqua dest. 3,58 g 0,136 g 8,77 g 9.1.2 Aufbereitung
SingleQuant Assay Kit
 GEBRAUCHSANLEITUNG SingleQuant Assay Kit Kit für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39226) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010
GEBRAUCHSANLEITUNG SingleQuant Assay Kit Kit für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39226) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010
Kapillarelektrophorese DNA-Sequenzierung
 Kapillarelektrophorese DNA-Sequenzierung DNA Kettenanalyse oder DNA-Sequenzierung wird bei der Anordnung der Primärstruktur und Bestimmung der Nukleotid-Basensequenz verwendet. Die Analyse basiert auf
Kapillarelektrophorese DNA-Sequenzierung DNA Kettenanalyse oder DNA-Sequenzierung wird bei der Anordnung der Primärstruktur und Bestimmung der Nukleotid-Basensequenz verwendet. Die Analyse basiert auf
Technische Universität Chemnitz Chemisches Grundpraktikum
 Technische Universität Chemnitz Chemisches Grundpraktikum Protokoll «CfP5 - Massanalytische Bestimmungsverfahren (Volumetrie)» Martin Wolf Betreuerin: Frau Sachse Datum:
Technische Universität Chemnitz Chemisches Grundpraktikum Protokoll «CfP5 - Massanalytische Bestimmungsverfahren (Volumetrie)» Martin Wolf Betreuerin: Frau Sachse Datum:
Tab. 2-1: TKZT-Zelllinien, Herkunft, histologische Eigenschaften und Referenzen
 Material 28 2 MATERIAL 2.1 Zelllinien In der vorliegenden Studie wurden etablierte Zelllinien von nichtseminomatösen TKZT untersucht. Die Untersuchungen wurden zunächst an den drei Zelllinien H12.1, 2102EP
Material 28 2 MATERIAL 2.1 Zelllinien In der vorliegenden Studie wurden etablierte Zelllinien von nichtseminomatösen TKZT untersucht. Die Untersuchungen wurden zunächst an den drei Zelllinien H12.1, 2102EP
Protokoll zur Übung Gelelektrophorese
 Protokoll zur Übung Gelelektrophorese im Rahmen des Praktikums Labor an der TU Wien Durchgeführt bei Univ.Ass. Mag.rer.nat. Dr.rer.nat. Martina Marchetti-Deschmann Verfasser des Protokolls: Gwendolin Korinek
Protokoll zur Übung Gelelektrophorese im Rahmen des Praktikums Labor an der TU Wien Durchgeführt bei Univ.Ass. Mag.rer.nat. Dr.rer.nat. Martina Marchetti-Deschmann Verfasser des Protokolls: Gwendolin Korinek
Entwicklung und Validierung von multiplex real-time RT-PCR assays in der Virusdiagnostik
 Entwicklung und Validierung von multiplex real-time RT-PCR assays in der Virusdiagnostik Bernd Hoffmann, Klaus R. Depner, Horst Schirrmeier & Martin Beer Friedrich-Loeffler-Institut Greifswald-Insel Riems
Entwicklung und Validierung von multiplex real-time RT-PCR assays in der Virusdiagnostik Bernd Hoffmann, Klaus R. Depner, Horst Schirrmeier & Martin Beer Friedrich-Loeffler-Institut Greifswald-Insel Riems
Bestimmung des Stickstoffgehalts von Erde
 Bestimmung des Stickstoffgehalts von Erde Schülerversuch, ca. 25 Minuten Experiment Teil 1 Material und Chemikalien: Ofentrockene Erde Kaliumchloridlösung (c = 2 mol/l) Flasche (250 ml) Trichter Filterpapier
Bestimmung des Stickstoffgehalts von Erde Schülerversuch, ca. 25 Minuten Experiment Teil 1 Material und Chemikalien: Ofentrockene Erde Kaliumchloridlösung (c = 2 mol/l) Flasche (250 ml) Trichter Filterpapier
Western-Blot Master-Anweisung, letzte Bearb. Feb 2014
 Western-Blot Master-Anweisung, letzte Bearb. Feb 2014 Proteintransfer (Handschuhe anziehen!) Behandlung der fertigen Gele: - Befülle 2 Schalen mit Transferpuffer (1 für die Gele, 1 für die Membranen) -
Western-Blot Master-Anweisung, letzte Bearb. Feb 2014 Proteintransfer (Handschuhe anziehen!) Behandlung der fertigen Gele: - Befülle 2 Schalen mit Transferpuffer (1 für die Gele, 1 für die Membranen) -
Datasheet. TriFaster Maximo Aufreinigung von DNA, RNA und Protein aus einer Probe
 TriFaster Maximo Aufreinigung von DNA, RNA und Protein aus einer Probe Features: - Extraktion von RNA, DNA und Proteinen aus der gleichen Probe - Für kleine und große Mengen von Probe - Gleichzeitiges
TriFaster Maximo Aufreinigung von DNA, RNA und Protein aus einer Probe Features: - Extraktion von RNA, DNA und Proteinen aus der gleichen Probe - Für kleine und große Mengen von Probe - Gleichzeitiges
peqgold TriFast FL Methode für die gleichzeitige Extraktion von RNA, DNA und Proteinen aus flüssigen Proben.
 peqgold TriFast FL Methode für die gleichzeitige Extraktion von RNA, DNA und Proteinen aus flüssigen Proben. Best.-Nr. 30-2110 100 ml 30-2120 200 ml 30-2130 500 ml Lagerung: Lichtgeschützt bei 4 C für
peqgold TriFast FL Methode für die gleichzeitige Extraktion von RNA, DNA und Proteinen aus flüssigen Proben. Best.-Nr. 30-2110 100 ml 30-2120 200 ml 30-2130 500 ml Lagerung: Lichtgeschützt bei 4 C für
Auf der Suche nach der Wundermedizin
 Auf der Suche nach der Wundermedizin Experimente im Schullabor 1 Herausgeber Novartis Pharma AG, CH-4002 Basel Autoren: Dr. Gesche Standke und Dr. Christiane Röckl Michel Zeichnungen: Fonds der Chemischen
Auf der Suche nach der Wundermedizin Experimente im Schullabor 1 Herausgeber Novartis Pharma AG, CH-4002 Basel Autoren: Dr. Gesche Standke und Dr. Christiane Röckl Michel Zeichnungen: Fonds der Chemischen
Sequenzierung. Aufklärung der Primärstruktur von DNA. Biotechnik Kurs WS 2006/07
 Sequenzierung Aufklärung der Primärstruktur von DNA Biotechnik Kurs WS 2006/07 AK Engels Angelika Keller Übersicht Geschichtlicher Hintergrund Maxam-Gilbert Sequenzierung Sanger Sequenzierung Neuere Sequenzierungstechnologien
Sequenzierung Aufklärung der Primärstruktur von DNA Biotechnik Kurs WS 2006/07 AK Engels Angelika Keller Übersicht Geschichtlicher Hintergrund Maxam-Gilbert Sequenzierung Sanger Sequenzierung Neuere Sequenzierungstechnologien
7. Bewässerung: Mehrmals pro Woche
 7. Bewässerung: Mehrmals pro Woche Eine Kultur im Erdboden muss mehrmals wöchentlich bewässert werden. 1. Erstellen Sie ein Arbeitsblatt 2. Pumpe 3. Ventilgruppe 1 4. Kulturfachregelung 5. Wasser-Anschlüsse
7. Bewässerung: Mehrmals pro Woche Eine Kultur im Erdboden muss mehrmals wöchentlich bewässert werden. 1. Erstellen Sie ein Arbeitsblatt 2. Pumpe 3. Ventilgruppe 1 4. Kulturfachregelung 5. Wasser-Anschlüsse
Informationsveranstaltung Heimtierfuttermittel. PCR-Analytik zur Bestimmung von GVOs in Heimtierfuttermitteln. C. Haldemann, ALP
 Informationsveranstaltung Heimtierfuttermittel PCR-Analytik zur Bestimmung von GVOs in Heimtierfuttermitteln C. Haldemann, ALP Grundidee des Nachweises von GVOs mittels PCR Die Bestimmung genveränderter
Informationsveranstaltung Heimtierfuttermittel PCR-Analytik zur Bestimmung von GVOs in Heimtierfuttermitteln C. Haldemann, ALP Grundidee des Nachweises von GVOs mittels PCR Die Bestimmung genveränderter
Typische Fragen für den Gehschul-Teil: Typ 1: Mengen und Konzentrationen:
 Die Gehschule ist ein Teil der Biochemischen Übungen für das Bakkalaureat LMBT. Aus organisatorischen Gründen wird dieser Test gleichzeitig mit der Prüfung aus Grundlagen der Biochemie angeboten. Das Abschneiden
Die Gehschule ist ein Teil der Biochemischen Übungen für das Bakkalaureat LMBT. Aus organisatorischen Gründen wird dieser Test gleichzeitig mit der Prüfung aus Grundlagen der Biochemie angeboten. Das Abschneiden
Produktinformation Saturn-2D REDOX Labeling Kit
 Saturn-2D REDOX Labeling Kit Produktinformation Saturn-2D REDOX Labeling Kit Produkt-Nr. PR34, PR35 NH DyeAGNOSTICS GmbH Weinbergweg 23 D-06120 Halle Deutschland Technischer Support Fon: +49 (0) 345-2799
Saturn-2D REDOX Labeling Kit Produktinformation Saturn-2D REDOX Labeling Kit Produkt-Nr. PR34, PR35 NH DyeAGNOSTICS GmbH Weinbergweg 23 D-06120 Halle Deutschland Technischer Support Fon: +49 (0) 345-2799
APP-GFP/Fluoreszenzmikroskop. Aufnahmen neuronaler Zellen, mit freund. Genehmigung von Prof. Stefan Kins, TU Kaiserslautern
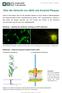 Über die Herkunft von Aβ42 und Amyloid-Plaques Heute ist sicher belegt, dass sich die amyloiden Plaques aus einer Vielzahl an Abbaufragmenten des Amyloid-Vorläufer-Proteins (amyloid-precursor-protein,
Über die Herkunft von Aβ42 und Amyloid-Plaques Heute ist sicher belegt, dass sich die amyloiden Plaques aus einer Vielzahl an Abbaufragmenten des Amyloid-Vorläufer-Proteins (amyloid-precursor-protein,
PCR-ELISA. Eine Methode zur Pathogendiagnose und zur Ermittlung der Befallsstärke
 PCR-ELISA Eine Methode zur Pathogendiagnose und zur Ermittlung der Befallsstärke Luitgardis Seigner und Stefan Knabel * Bayerische Landesanstalt für Landwirtschaft Institut für Pflanzenschutz * Ehemaliger
PCR-ELISA Eine Methode zur Pathogendiagnose und zur Ermittlung der Befallsstärke Luitgardis Seigner und Stefan Knabel * Bayerische Landesanstalt für Landwirtschaft Institut für Pflanzenschutz * Ehemaliger
Das Reagenz speziell für die Transfektion von Säugerzellen mit sirna und mirna
 METAFECTENE SI + Das Reagenz speziell für die Transfektion von Säugerzellen mit sirna und mirna Bestellinformationen, MSDS, Publikationen und Anwendungsbeispiele unter www.biontex.com Produkt Katalognummer
METAFECTENE SI + Das Reagenz speziell für die Transfektion von Säugerzellen mit sirna und mirna Bestellinformationen, MSDS, Publikationen und Anwendungsbeispiele unter www.biontex.com Produkt Katalognummer
Färbung mit AzurGel-K
 Arbeitsanleitung zur Färbung mit AzurGel-K für Gele im Format 10 x 10 x 0,1 cm Kat. Nr.: GF 10002 Ringstr. 4 64401 Gross-Bieberau Tel. ++49-6162-809840 Fax ++49-6162-8098420 www.anamed-gele.com Grundlage
Arbeitsanleitung zur Färbung mit AzurGel-K für Gele im Format 10 x 10 x 0,1 cm Kat. Nr.: GF 10002 Ringstr. 4 64401 Gross-Bieberau Tel. ++49-6162-809840 Fax ++49-6162-8098420 www.anamed-gele.com Grundlage
Quantitative Analytik -231- Elektrophorese. Bei dieser Gruppe von Methoden werden Ionen durch Anlegen eines elektrischen Feldes transportiert.
 Quantitative Analytik -231- Elektrophorese 9. ELEKTROPHORESE Bei dieser Gruppe von Methoden werden Ionen durch Anlegen eines elektrischen Feldes transportiert. Elektrophoretische Mobilität von Ionen in
Quantitative Analytik -231- Elektrophorese 9. ELEKTROPHORESE Bei dieser Gruppe von Methoden werden Ionen durch Anlegen eines elektrischen Feldes transportiert. Elektrophoretische Mobilität von Ionen in
Professionelle Seminare im Bereich MS-Office
 Der Name BEREICH.VERSCHIEBEN() ist etwas unglücklich gewählt. Man kann mit der Funktion Bereiche zwar verschieben, man kann Bereiche aber auch verkleinern oder vergrößern. Besser wäre es, die Funktion
Der Name BEREICH.VERSCHIEBEN() ist etwas unglücklich gewählt. Man kann mit der Funktion Bereiche zwar verschieben, man kann Bereiche aber auch verkleinern oder vergrößern. Besser wäre es, die Funktion
Restriktion zweier Plasmide zur Erstellung einer physikalischen Karte, Grundlagen der DNA- Trennung und Analyse über Agarosegele
 Versuch 1: Restriktionsenzyme als molekulare Werkzeuge Versuchsinhalt Restriktion zweier Plasmide zur Erstellung einer physikalischen Karte, Grundlagen der DNA- Trennung und Analyse über Agarosegele Zwei
Versuch 1: Restriktionsenzyme als molekulare Werkzeuge Versuchsinhalt Restriktion zweier Plasmide zur Erstellung einer physikalischen Karte, Grundlagen der DNA- Trennung und Analyse über Agarosegele Zwei
Nachweis von DNA im Wein
 Abschlussbericht über den Forschungsauftrag Nachweis von DNA im Wein Projektlaufzeit: 01.01.2001 bis 31.03.2003 Prof. Dr. Ralf Kaldenhoff Universität Würzburg Julius-von-Sachs-Institut für Biowissenschaften
Abschlussbericht über den Forschungsauftrag Nachweis von DNA im Wein Projektlaufzeit: 01.01.2001 bis 31.03.2003 Prof. Dr. Ralf Kaldenhoff Universität Würzburg Julius-von-Sachs-Institut für Biowissenschaften
4.5. Ergebnisse der Expression und Aufreinigung von rekombinanten Proteinen aus Escherichia coli
 4.5. Ergebnisse der Expression und Aufreinigung von rekombinanten Proteinen aus Escherichia coli Für die Auswertung des ELISAs wurden Positivkontrollen benötigt. Dazu wurde einem Teil der Tiere subcutan
4.5. Ergebnisse der Expression und Aufreinigung von rekombinanten Proteinen aus Escherichia coli Für die Auswertung des ELISAs wurden Positivkontrollen benötigt. Dazu wurde einem Teil der Tiere subcutan
4.1. Herstellung des CH2/CH3-trunkierten dimerisierten anti-cd30-igg1-tnf- Fusionsproteins
 ERGEBNISSE 29 4. Ergebnisse 4.1. Herstellung des CH2/CH3-trunkierten dimerisierten anti-cd3-igg1-tnf- Fusionsproteins Im vorliegenden Immunzytokin wurden die Domänen CH2/CH3 des humanen Fc-Fragmentes durch
ERGEBNISSE 29 4. Ergebnisse 4.1. Herstellung des CH2/CH3-trunkierten dimerisierten anti-cd3-igg1-tnf- Fusionsproteins Im vorliegenden Immunzytokin wurden die Domänen CH2/CH3 des humanen Fc-Fragmentes durch
AZK 1- Freistil. Der Dialog "Arbeitszeitkonten" Grundsätzliches zum Dialog "Arbeitszeitkonten"
 AZK 1- Freistil Nur bei Bedarf werden dafür gekennzeichnete Lohnbestandteile (Stundenzahl und Stundensatz) zwischen dem aktuellen Bruttolohnjournal und dem AZK ausgetauscht. Das Ansparen und das Auszahlen
AZK 1- Freistil Nur bei Bedarf werden dafür gekennzeichnete Lohnbestandteile (Stundenzahl und Stundensatz) zwischen dem aktuellen Bruttolohnjournal und dem AZK ausgetauscht. Das Ansparen und das Auszahlen
Alternative Methoden der RNA-Analyse
 Alternative Methoden der RNA-Analyse In diesem Versuch wurde die Northern Blot Hybridisierung zur Analyse isolierter mrna eingesetzt. Mit dieser Technik können Größe und Menge einer spezifischen RNA bestimmt
Alternative Methoden der RNA-Analyse In diesem Versuch wurde die Northern Blot Hybridisierung zur Analyse isolierter mrna eingesetzt. Mit dieser Technik können Größe und Menge einer spezifischen RNA bestimmt
Überprüfung der digital signierten E-Rechnung
 Überprüfung der digital signierten E-Rechnung Aufgrund des BMF-Erlasses vom Juli 2005 (BMF-010219/0183-IV/9/2005) gelten ab 01.01.2006 nur noch jene elektronischen Rechnungen als vorsteuerabzugspflichtig,
Überprüfung der digital signierten E-Rechnung Aufgrund des BMF-Erlasses vom Juli 2005 (BMF-010219/0183-IV/9/2005) gelten ab 01.01.2006 nur noch jene elektronischen Rechnungen als vorsteuerabzugspflichtig,
PharmaResearch. Analyse des Pressvorgangs. Mehr als Forschung und Entwicklung
 PharmaResearch Analyse des Pressvorgangs Mehr als Forschung und Entwicklung Unterstützung für die Entwicklung PharmaResearch erfasst und wertet sämtliche Prozessdaten von instrumentierten Tablettenpressen
PharmaResearch Analyse des Pressvorgangs Mehr als Forschung und Entwicklung Unterstützung für die Entwicklung PharmaResearch erfasst und wertet sämtliche Prozessdaten von instrumentierten Tablettenpressen
LED Beleuchtung - Fehlerbetrachtung bei der Beleuchtungsstärkemessung
 LED Beleuchtung - Fehlerbetrachtung bei der Beleuchtungsstärkemessung Bei einem Beleuchtungsstärkemessgerät ist eines der wichtigsten Eigenschaften die Anpassung an die Augenempfindlichkeit V(λ). V(λ)
LED Beleuchtung - Fehlerbetrachtung bei der Beleuchtungsstärkemessung Bei einem Beleuchtungsstärkemessgerät ist eines der wichtigsten Eigenschaften die Anpassung an die Augenempfindlichkeit V(λ). V(λ)
Säure-Base-Titrationen
 Säure-Base-Titrationen Dieses Skript gehört: Säure Base - Titrationen Seite 2 Hinweis: Mit den Säuren und Basen ist vorsichtig umzugehen, um Verätzungen zu vermeiden! Versuch 1: Herstellen einer Natronlauge
Säure-Base-Titrationen Dieses Skript gehört: Säure Base - Titrationen Seite 2 Hinweis: Mit den Säuren und Basen ist vorsichtig umzugehen, um Verätzungen zu vermeiden! Versuch 1: Herstellen einer Natronlauge
Wasserchemie Modul 7
 Wasserchemie Modul 7 Prinzip eines heterogenen Enzyme ELISA Enzyme Linked Immuno Sorbent Assay Was sind Antikörper Antikörper (Immunoglobuline) sind Eiweißstoffe stoffe,, die Tiere und Menschen zur Abwehr
Wasserchemie Modul 7 Prinzip eines heterogenen Enzyme ELISA Enzyme Linked Immuno Sorbent Assay Was sind Antikörper Antikörper (Immunoglobuline) sind Eiweißstoffe stoffe,, die Tiere und Menschen zur Abwehr
Biochemisches Grundpraktikum
 Biochemisches Grundpraktikum Versuch Nummer G-01 01: Potentiometrische und spektrophotometrische Bestim- mung von Ionisationskonstanten Gliederung: I. Titrationskurve von Histidin und Bestimmung der pk-werte...
Biochemisches Grundpraktikum Versuch Nummer G-01 01: Potentiometrische und spektrophotometrische Bestim- mung von Ionisationskonstanten Gliederung: I. Titrationskurve von Histidin und Bestimmung der pk-werte...
Skript zum Praktikum Instrumentelle Analytik der Universität Heidelberg im 4. Fachsemester Pharmazie
 HPLC 1 Skript zum Praktikum Instrumentelle Analytik der Universität Heidelberg im 4. Fachsemester Pharmazie 1. Aufgabe In diesem Versuch werden die Retentionszeiten der Substanzen Acetylsalicylsäure (ASS)
HPLC 1 Skript zum Praktikum Instrumentelle Analytik der Universität Heidelberg im 4. Fachsemester Pharmazie 1. Aufgabe In diesem Versuch werden die Retentionszeiten der Substanzen Acetylsalicylsäure (ASS)
E-MAIL VERWALTUNG. Postfächer, Autoresponder, Weiterleitungen, Aliases. http://www.athost.at. Bachstraße 47, 3580 Mödring office@athost.
 E-MAIL VERWALTUNG Postfächer, Autoresponder, Weiterleitungen, Aliases http://www.athost.at Bachstraße 47, 3580 Mödring office@athost.at Loggen Sie sich zunächst unter http://www.athost.at/kundencenter
E-MAIL VERWALTUNG Postfächer, Autoresponder, Weiterleitungen, Aliases http://www.athost.at Bachstraße 47, 3580 Mödring office@athost.at Loggen Sie sich zunächst unter http://www.athost.at/kundencenter
Die RT-PCR Untersuchungen wurden anhand 27 Struma nodosa- (siehe Tab. 7) und 15 Adenom- (siehe Tab. 11) Präparaten durchgeführt.
 - 22-4 Ergebnisse 4.1 RT-PCR Die RT-PCR Untersuchungen wurden anhand 27 Struma nodosa- (siehe Tab. 7) und 15 Adenom- (siehe Tab. 11) Präparaten durchgeführt. 4.1.1 Struma nodosa Histologie Fas Fas CD 97
- 22-4 Ergebnisse 4.1 RT-PCR Die RT-PCR Untersuchungen wurden anhand 27 Struma nodosa- (siehe Tab. 7) und 15 Adenom- (siehe Tab. 11) Präparaten durchgeführt. 4.1.1 Struma nodosa Histologie Fas Fas CD 97
Transferpuffer und allgemeine Tipps für Blotting-Ansätze
 Transferpuffer und allgemeine Tipps für Blotting-Ansätze Transferpuffer für Semi-Dry-Blotting Im Semi-Dry-Blotting-System kann man sowohl ein kontinuierliches Puffersystem (identischer Puffer an Anode
Transferpuffer und allgemeine Tipps für Blotting-Ansätze Transferpuffer für Semi-Dry-Blotting Im Semi-Dry-Blotting-System kann man sowohl ein kontinuierliches Puffersystem (identischer Puffer an Anode
Molekulargenetische Experimente IV: Plasmidpräparation
 Molekulargenetische Experimente IV: Plasmidpräparation Plasmide sind kleine, ringförmige DNA-Moleküle in Bakterien, die in der Lage sind, sich selbst mit Hilfe von Enzymen zu replizieren. Gene, die auf
Molekulargenetische Experimente IV: Plasmidpräparation Plasmide sind kleine, ringförmige DNA-Moleküle in Bakterien, die in der Lage sind, sich selbst mit Hilfe von Enzymen zu replizieren. Gene, die auf
Abkürzungsverzeichnis... 7. Inhaltsverzeichnis... 11. Abbildungsverzeichnis... 17. 1 Einleitung... 21 1.1 Proteomik... 21 1.1.1 Proteom...
 Inhaltsverzeichnis Abkürzungsverzeichnis... 7 Inhaltsverzeichnis... 11 Abbildungsverzeichnis... 17 1 Einleitung... 21 1.1 Proteomik... 21 1.1.1 Proteom... 21 1.1.2 Protein-Protein Interaktionen allgemein...
Inhaltsverzeichnis Abkürzungsverzeichnis... 7 Inhaltsverzeichnis... 11 Abbildungsverzeichnis... 17 1 Einleitung... 21 1.1 Proteomik... 21 1.1.1 Proteom... 21 1.1.2 Protein-Protein Interaktionen allgemein...
Behaglichkeitsmessung mit neuem Messgerät 435 von testo AG
 Behaglichkeitsmessung mit neuem Messgerät 435 von testo AG Die zuvor besuchte Schulung in Lenzkirch behandelte das testo Behaglichkeitsmessgerät 480. Die von dem beiden Regio-Teams verwendeten Geräte gehören
Behaglichkeitsmessung mit neuem Messgerät 435 von testo AG Die zuvor besuchte Schulung in Lenzkirch behandelte das testo Behaglichkeitsmessgerät 480. Die von dem beiden Regio-Teams verwendeten Geräte gehören
DNA-Sequenzierung. Martina Krause
 DNA-Sequenzierung Martina Krause Inhalt Methoden der DNA-Sequenzierung Methode nach Maxam - Gilbert Methode nach Sanger Einleitung Seit 1977 stehen zwei schnell arbeitende Möglichkeiten der Sequenzanalyse
DNA-Sequenzierung Martina Krause Inhalt Methoden der DNA-Sequenzierung Methode nach Maxam - Gilbert Methode nach Sanger Einleitung Seit 1977 stehen zwei schnell arbeitende Möglichkeiten der Sequenzanalyse
Säure-Base Titrationen. (Seminar zu den Übungen zur quantitativen Bestimmung von Arznei-, Hilfs- und Schadstoffen)
 Säure-Base Titrationen (Seminar zu den Übungen zur quantitativen Bestimmung von Arznei-, Hilfs- und Schadstoffen) 1. Gehaltsbestimmung von Salzsäure HCl ist eine starke Säure (fast zu 100% dissoziiert)
Säure-Base Titrationen (Seminar zu den Übungen zur quantitativen Bestimmung von Arznei-, Hilfs- und Schadstoffen) 1. Gehaltsbestimmung von Salzsäure HCl ist eine starke Säure (fast zu 100% dissoziiert)
Persönliches Adressbuch
 Persönliches Adressbuch Persönliches Adressbuch Seite 1 Persönliches Adressbuch Seite 2 Inhaltsverzeichnis 1. WICHTIGE INFORMATIONEN ZUR BEDIENUNG VON CUMULUS 4 2. ALLGEMEINE INFORMATIONEN ZUM PERSÖNLICHEN
Persönliches Adressbuch Persönliches Adressbuch Seite 1 Persönliches Adressbuch Seite 2 Inhaltsverzeichnis 1. WICHTIGE INFORMATIONEN ZUR BEDIENUNG VON CUMULUS 4 2. ALLGEMEINE INFORMATIONEN ZUM PERSÖNLICHEN
Teilnahme am Apple ios Developer Program
 Teilnahme am Apple ios Developer Program D-U-N-S-Nummer Für die Anmeldung als Firma brauchen Sie zunächst eine so genannte D-U-N-S-Nummer. Mehr Informationen zu dieser Nummer finden Sie unter http://de.wikipedia.org/wiki/d-u-n-s.
Teilnahme am Apple ios Developer Program D-U-N-S-Nummer Für die Anmeldung als Firma brauchen Sie zunächst eine so genannte D-U-N-S-Nummer. Mehr Informationen zu dieser Nummer finden Sie unter http://de.wikipedia.org/wiki/d-u-n-s.
HOWTO Update von MRG1 auf MRG2 bei gleichzeitigem Update auf Magento CE 1.4 / Magento EE 1.8
 Update von MRG1 auf MRG2 bei gleichzeitigem Update auf Magento CE 1.4 / Magento EE 1.8 Schritt 1: Altes Modul-Paket vollständig deinstallieren Die neuen MRG-Module sind aus dem Scope local in den Scope
Update von MRG1 auf MRG2 bei gleichzeitigem Update auf Magento CE 1.4 / Magento EE 1.8 Schritt 1: Altes Modul-Paket vollständig deinstallieren Die neuen MRG-Module sind aus dem Scope local in den Scope
2 Material und Methoden
 2 Material und Methoden 2.1 Material 2.1.1 Allgemeine Chemikalien Alle verwendeten Chemikalien wurden in der Qualität pro analysis (p.a.) eingesetzt. Allgemeine Chemikalien und Verbrauchsmaterialien und
2 Material und Methoden 2.1 Material 2.1.1 Allgemeine Chemikalien Alle verwendeten Chemikalien wurden in der Qualität pro analysis (p.a.) eingesetzt. Allgemeine Chemikalien und Verbrauchsmaterialien und
5,6- Carboxy- Rhodamin (Rox) TIB MolBiol, Berlin Desoxynukleosidtriphosphat (dntp)
 8 Anhang 8.1 Chemikalien und Reagenzien Bromphenolblau Bromma, Schweden 5,6- Carboxy- Rhodamin (Rox) TIB MolBiol, Berlin Desoxynukleosidtriphosphat (dntp) Invitrogen TM, Karlsruhe Ethanol (RNase-frei)
8 Anhang 8.1 Chemikalien und Reagenzien Bromphenolblau Bromma, Schweden 5,6- Carboxy- Rhodamin (Rox) TIB MolBiol, Berlin Desoxynukleosidtriphosphat (dntp) Invitrogen TM, Karlsruhe Ethanol (RNase-frei)
PCR (polymerase chain reaction)
 PCR (polymerase chain reaction) Ist ein in vitro Verfahren zur selektiven Anreicherung von Nukleinsäure-Bereichen definierter Länge und definierter Sequenz aus einem Gemisch von Nukleinsäure-Molekülen
PCR (polymerase chain reaction) Ist ein in vitro Verfahren zur selektiven Anreicherung von Nukleinsäure-Bereichen definierter Länge und definierter Sequenz aus einem Gemisch von Nukleinsäure-Molekülen
Anorganisches Praktikum 1. Semester. FB Chemieingenieurwesen. Labor für Anorg. Chemie Angew. Materialwiss. Versuchsvorschriften
 Anorganisches Praktikum 1. Semester FB Chemieingenieurwesen Labor für Anorg. Chemie Angew. Materialwiss. Versuchsvorschriften 1 Gravimetrie Bestimmung von Nickel Sie erhalten eine Lösung, die 0.1-0.2g
Anorganisches Praktikum 1. Semester FB Chemieingenieurwesen Labor für Anorg. Chemie Angew. Materialwiss. Versuchsvorschriften 1 Gravimetrie Bestimmung von Nickel Sie erhalten eine Lösung, die 0.1-0.2g
Subpostfächer und Vertretungen für Unternehmen
 SCHRITT-FÜR-SCHRITT Seite 1 von 7 Subpostfächer und Vertretungen für Unternehmen Organisationsstruktur 1:1 abbilden Individuelle Postfächer für Abteilungen und/oder Mitarbeiter Unterschiedliche Berechtigungen
SCHRITT-FÜR-SCHRITT Seite 1 von 7 Subpostfächer und Vertretungen für Unternehmen Organisationsstruktur 1:1 abbilden Individuelle Postfächer für Abteilungen und/oder Mitarbeiter Unterschiedliche Berechtigungen
1. PCR Polymerase-Kettenreaktion
 entechnische Verfahren 1. PCR Polymerase-Kettenreaktion Die PCR (engl. Polymerase Chain Reaction) ist eine Methode, um die DNA zu vervielfältigen, ohne einen lebenden Organismus, wie z.b. Escherichia coli
entechnische Verfahren 1. PCR Polymerase-Kettenreaktion Die PCR (engl. Polymerase Chain Reaction) ist eine Methode, um die DNA zu vervielfältigen, ohne einen lebenden Organismus, wie z.b. Escherichia coli
Versuch: Siedediagramm eines binären Gemisches
 Versuch: Siedediagramm eines binären Gemisches Aufgaben - Kalibriermessungen Bestimmen Sie experimentell den Brechungsindex einer gegebenen Mischung bei unterschiedlicher Zusammensetzung. - Theoretische
Versuch: Siedediagramm eines binären Gemisches Aufgaben - Kalibriermessungen Bestimmen Sie experimentell den Brechungsindex einer gegebenen Mischung bei unterschiedlicher Zusammensetzung. - Theoretische
SERVA Lightning Sci2. SERVA Lightning Sci3. SERVA Lightning Sci5. SERVA Lightning SciDye Set
 GEBRAUCHSANLEITUNG SERVA Lightning Sci2 (Kat.-Nr. 43404) SERVA Lightning Sci3 (Kat.-Nr. 43405) SERVA Lightning Sci5 (Kat.-Nr. 43406) SERVA Lightning SciDye Set (Kat.-Nr. 43407) Fluoreszenzfarbstoffe für
GEBRAUCHSANLEITUNG SERVA Lightning Sci2 (Kat.-Nr. 43404) SERVA Lightning Sci3 (Kat.-Nr. 43405) SERVA Lightning Sci5 (Kat.-Nr. 43406) SERVA Lightning SciDye Set (Kat.-Nr. 43407) Fluoreszenzfarbstoffe für
GEVITAS Farben-Reaktionstest
 GEVITAS Farben-Reaktionstest GEVITAS Farben-Reaktionstest Inhalt 1. Allgemeines... 1 2. Funktionsweise der Tests... 2 3. Die Ruhetaste und die Auslösetaste... 2 4. Starten der App Hauptmenü... 3 5. Auswahl
GEVITAS Farben-Reaktionstest GEVITAS Farben-Reaktionstest Inhalt 1. Allgemeines... 1 2. Funktionsweise der Tests... 2 3. Die Ruhetaste und die Auslösetaste... 2 4. Starten der App Hauptmenü... 3 5. Auswahl
Gentechnologie: Isolierung und Charakterisierung von DNA
 Genetisches Grundpraktikum 9. Kurstag 23.06.2005 Gentechnologie: Isolierung und Charakterisierung von DNA Lerninhalte: Klonierung, Plasmid, Polylinker ( multiple cloning site ), Restriktionsendonuklease,
Genetisches Grundpraktikum 9. Kurstag 23.06.2005 Gentechnologie: Isolierung und Charakterisierung von DNA Lerninhalte: Klonierung, Plasmid, Polylinker ( multiple cloning site ), Restriktionsendonuklease,
. = Standardabweichung, berechnet aus Ergebnissen, die unter Vergleichsbedingungen erhalten worden sind.
 RESOLUTION OIV/OENO 427/2010 Geändert Durch OIV-COMEX 502-2012 1 Definitionen der Verfahrenskriterien Richtigkeit r = Grad der Übereinstimmung zwischen dem aus einer großen Serie von Testergebnissen erhaltenen
RESOLUTION OIV/OENO 427/2010 Geändert Durch OIV-COMEX 502-2012 1 Definitionen der Verfahrenskriterien Richtigkeit r = Grad der Übereinstimmung zwischen dem aus einer großen Serie von Testergebnissen erhaltenen
Erstellen von x-y-diagrammen in OpenOffice.calc
 Erstellen von x-y-diagrammen in OpenOffice.calc In dieser kleinen Anleitung geht es nur darum, aus einer bestehenden Tabelle ein x-y-diagramm zu erzeugen. D.h. es müssen in der Tabelle mindestens zwei
Erstellen von x-y-diagrammen in OpenOffice.calc In dieser kleinen Anleitung geht es nur darum, aus einer bestehenden Tabelle ein x-y-diagramm zu erzeugen. D.h. es müssen in der Tabelle mindestens zwei
www.gbo.com/bioscience Gewebekultur 1 Zell- und Microplatten 2 HTS- 3 Immunologie/ HLA 4 Mikrobiologie/ Bakteriologie Mehrzweckgefäße 5 Röhrchen/
 13 Reaktions/ 2 HTS 1 Zell und Reaktionsgefäße für die PCR 7 I 2 PCR Tubes 7 I 2 PCR 8er Streifen 7 I 3 PCR 7 I 4 Polypropylen 7 I 4 384 Well Polypropylen 7 I 4 PCR Kompatibilitätstabelle 7 I 6 ThermoQuick
13 Reaktions/ 2 HTS 1 Zell und Reaktionsgefäße für die PCR 7 I 2 PCR Tubes 7 I 2 PCR 8er Streifen 7 I 3 PCR 7 I 4 Polypropylen 7 I 4 384 Well Polypropylen 7 I 4 PCR Kompatibilitätstabelle 7 I 6 ThermoQuick
14. Minimale Schichtdicken von PEEK und PPS im Schlauchreckprozeß und im Rheotensversuch
 14. Minimale Schichtdicken von PEEK und PPS im Schlauchreckprozeß und im Rheotensversuch Analog zu den Untersuchungen an LDPE in Kap. 6 war zu untersuchen, ob auch für die Hochtemperatur-Thermoplaste aus
14. Minimale Schichtdicken von PEEK und PPS im Schlauchreckprozeß und im Rheotensversuch Analog zu den Untersuchungen an LDPE in Kap. 6 war zu untersuchen, ob auch für die Hochtemperatur-Thermoplaste aus
teamspace TM Outlook Synchronisation
 teamspace TM Outlook Synchronisation Benutzerhandbuch teamsync Version 1.4 Stand Dezember 2005 * teamspace ist ein eingetragenes Markenzeichen der 5 POINT AG ** Microsoft Outlook ist ein eingetragenes
teamspace TM Outlook Synchronisation Benutzerhandbuch teamsync Version 1.4 Stand Dezember 2005 * teamspace ist ein eingetragenes Markenzeichen der 5 POINT AG ** Microsoft Outlook ist ein eingetragenes
RESOLUTION OENO 24/2004 NACHWEIS VON EIWEISSSTOFFEN PFLANZLICHER HERKUNFT IN WEIN UND MOST
 NACHWEIS VON EIWEISSSTOFFEN PFLANZLICHER HERKUNFT IN WEIN UND MOST DIE GENERALVERSAMMLUNG, unter Bezugnahme auf Artikel 2, Paragraf 2 IV des Gründungsübereinkommens vom 3. April 2001 der Internationalen
NACHWEIS VON EIWEISSSTOFFEN PFLANZLICHER HERKUNFT IN WEIN UND MOST DIE GENERALVERSAMMLUNG, unter Bezugnahme auf Artikel 2, Paragraf 2 IV des Gründungsübereinkommens vom 3. April 2001 der Internationalen
Installation OMNIKEY 3121 USB
 Installation OMNIKEY 3121 USB Vorbereitungen Installation PC/SC Treiber CT-API Treiber Einstellungen in Starke Praxis Testen des Kartenlesegeräts Vorbereitungen Bevor Sie Änderungen am System vornehmen,
Installation OMNIKEY 3121 USB Vorbereitungen Installation PC/SC Treiber CT-API Treiber Einstellungen in Starke Praxis Testen des Kartenlesegeräts Vorbereitungen Bevor Sie Änderungen am System vornehmen,
Dieser Ablauf soll eine Hilfe für die tägliche Arbeit mit der SMS Bestätigung im Millennium darstellen.
 Millennium SMS Service Schnellübersicht Seite 1 von 6 1. Tägliche Arbeiten mit der SMS Bestätigung Dieser Ablauf soll eine Hilfe für die tägliche Arbeit mit der SMS Bestätigung im Millennium darstellen.
Millennium SMS Service Schnellübersicht Seite 1 von 6 1. Tägliche Arbeiten mit der SMS Bestätigung Dieser Ablauf soll eine Hilfe für die tägliche Arbeit mit der SMS Bestätigung im Millennium darstellen.
