Einleitende Referate Keynote presentation
|
|
|
- Uwe Ursler
- vor 8 Jahren
- Abrufe
Transkript
1 Einleitende Referate Keynote presentation Neue molekularbiologische und bioinformatische Methoden in der Unkrautforschung New molecular biology and bioinformatics methods in weed research Antje Krause Fachhochschule Bingen, Berlinstr. 109, D Bingen am Rhein DOI /jka Zusammenfassung Der zunehmende Einsatz kostengünstiger und zeitsparender Hochdurchsatz-Sequenziertechniken (NGS, nextgeneration sequencing) ermöglicht die Bearbeitung völlig neuer Fragestellungen sowohl in der Medizin als auch in den Agrarwissenschaften. Die Verfügbarkeit von immer mehr genetischen Daten verschiedener Spezies und der Einsatz neuer molekularbiologischer und bioinformatischer Methoden zu ihrer Verarbeitung verschiebt damit den Blick von einzelnen Genen und Genprodukten hin zum Verständnis von Reaktionen, Interaktionen und ganzen biologischen Systemen. Damit sind auch ihre Einsatzmöglichkeiten in der Unkrautforschung vielfältig. Untersuchungen des Genoms und Transkriptoms eines Unkrauts können z. B. bei der Identifikation von Genprodukten, die als Zielorte (target-sites) für Herbizide geeignet sind, eingesetzt werden. Genexpressionsanalysen tragen zu einem besseren Verständnis von Herbizidresistenzen (sowohl Zielort- als auch Nicht-Zielortresistenzen) bei. Ferner kann die Sequenzierung des Metagenoms Aufschlüsse über mögliche Interaktionen mit Pflanzen- Mikroorganismen am untersuchten Standort geben. Stichwörter: Biologische Datenbanken, Bioinformatik, Epigenetik, Exom, Expressionsdatenanalyse, Genom, Hochdurchsatz-Sequenzierung, Transkriptom Abstract The application of time and cost efficient high-throughput sequencing technologies called NGS, nextgeneration sequencing enables researchers to tackle completely new problems in medicine as well as in agriculture. The availability of increasing genetics data from various species along with the use of new molecular biology and bioinformatics methods for data handling shifts the focus from single genes or gene products to the understanding of reactions, interactions and entire biological systems. In weed research the application of these methods is straightforward. The analysis of the genome and transcriptome of a weed can, for instance, lead to the identification of suitable gene products as target-sites for herbicides. Gene expression analyses result in a deeper understanding of herbicide resistance (target-site as well as non target-site resistance). In addition, sequencing the metagenome provides insights into potential interactions with microorganisms in the habitat of interest. Keywords: Biological databases, bioinformatics, epigenetics, exome, expression analysis, genome, nextgeneration sequencing, transcriptome Einleitung Seit der kompletten Genom-Sequenzierung des pflanzlichen Modellorganismus Arabidopsis thaliana im Jahr 2000 (THE ARABIDOPSIS GENOME INITIATIVE, 2000) und der ersten Nutzpflanze Oryza sativa im Jahr 2002 (GOFF et al., 2002) gewinnt die Analyse von genetischen Informationen zunehmend auch in der Pflanzenforschung an Bedeutung. Eine ganze Reihe neuer molekularbiologischer und bioinformatischer Methoden hat diese Entwicklung erst möglich gemacht. Julius-Kühn-Archiv, 443,
2 26. Deutsche Arbeitsbesprechung über Fragen der Unkrautbiologie und -bekämpfung, März 2014 in Braunschweig Unter dem Begriff Next Generation Sequencing (NGS) werden insbesondere neue Hochdurchsatz-Sequenziertechniken zusammengefasst, die es aufgrund einer Parallelisierung bzw. Miniaturisierung der Sequenzierung ermöglichen, DNA mit einem sehr guten Zeit-Kosten- Verhältnis zu sequenzieren. So lagen die Kosten zur Sequenzierung von Basenpaaren (1 Mbp) im April 2013 bei 0,06$ im Vergleich zu über 5.000$ im September 2001 (WETTERSTRAND, 2013). Hierbei wird unterschieden zwischen Sequenziergeräten, die eine Amplifizierung (d.h. Vervielfältigung, üblicherweise mit PCR (Polymerase Chain Reaction)) der zu sequenzierenden DNA voraussetzen (Amplified Single Molecule Sequencing, Second oder Next Generation Sequencing) und solchen, die einzelne DNA-Stränge ohne vorherige Amplifizierung sequenzieren (Single Molecule Sequencing, Third oder Next Next Generation Sequencing). Eine Übersicht über die aktuellen Technologien findet sich in Tabelle 1. Mit diesen Sequenziergeräten können in sehr kurzer Zeit (wenige Stunden) sehr große Mengen (mehrere Terabyte) an DNA- (Genom) bzw. mrna-daten (Transkriptom) für weitere Analysen in digitaler Form in den Computer gebracht werden. Diese Rohdaten werden dann dort mit Methoden der Bioinformatik weiter verarbeitet. Tab. 1 Hochdurchsatz-Sequenziertechniken; NGS: Next Generation Sequencing, Second Generation Sequencing, Amplified Single Molecule Sequencing; NNGS: Next Next Generation Sequencing, Third Generation Sequencing, Single Molecule Sequencing. Tab. 1 High-throughput sequencing technologies. Hersteller Webseite Generation Gerät(e) 454 Sequencing, NGS GS Junior Roche GS FLX+ Illumina NGS HiSeq 2500 GAIIx Applied Biosystems, Life Technologies Ion Torrent, Life Technologies NGS 5500xl SOLiD NGS Ion PGM Ion Proton Readlänge (in bp) Reads pro Lauf Mio. 3 Mrd. 320 Mio Mio Pacific Biosciences NNGS RS II Max. > Oxford Nanopore Technologies Geräte noch nicht auf dem Markt NNGS GridION MinION 2-3 Mio Mio ? 2.000? Da die meisten NGS-Sequenziergeräte nur sehr kurze Sequenzfragmente (Reads) produzieren und diese fehlerbehaftet sein können, ist die erste Herausforderung das Zusammenfügen dieser Fragmente zu größeren Sequenzabschnitten. Jede Position der zu rekonstruierenden Sequenz wird dabei idealerweise von mehreren Reads abgedeckt (Coverage), sodass die Reads allein aufgrund ihrer Ähnlichkeiten, d.h. ihres Überlapps (Overlap), untereinander zu einem größeren Sequenzabschnitt (Contig, Contiguous sequence) zusammengefügt werden können. Bei diesem Assembly genannten Prozess kann grob zwischen zwei Problemstellungen unterschieden werden: Beim Mapping werden die Reads in Übereinstimmung mit einem vorgegebenen bekannten Template gebracht. Dies kann ein bereits sequenziertes Genom, Transkriptom oder Exom derselben oder einer möglichst nah verwandten Spezies sein. Bei der de-novo- Assemblierung ist dagegen nichts über die Zielsequenz bekannt. Für einen aktuellen Überblick über Assemblierungsmethoden siehe NAGARAJAN und POP (2013). 18 Julius-Kühn-Archiv, 443, 2014
3 Erst nach der Assemblierung kann die eigentliche Analyse der Sequenzen am Computer erfolgen. Tabelle 2 listet die wichtigsten Datensammlungen mit Ergebnissen aus öffentlichen Pflanzengenomprojekten auf. Tab. 2 Pflanzengenetische Datensammlungen. Tab. 2 Plant genetics databases. Name Webseite Literatur The Arabidopsis Information Resource (LAMESCH et al., 2012) (TAIR) Ensembl plants (FLICEK et al., 2013) MIPS Plants DB (NUSSBAUMER et al., 2013) Gramene (YOUENS-CLARK et al., 2011) Phytozome (GOODSTEIN et al., 2012) Brachypodium distachyon (THE INTERNATIONAL BRACHYPODIUM INITIATIVE, 2010) PlantGDB (DUVICK et al., 2008) PlantCYC / Plant Metabolic Network (PMN) 1001 Genomes - A Catalog of Arabidopsis thaliana Genetic Variation (ZHANG et al., 2010) (CAO et al., 2011) Anwendungsgebiete Im Folgenden sollen die einzelnen Methoden zur Analyse von Genom, Metagenom, Exom, Transkriptom, Metabolom und Epigenom näher betrachtet werden. Genom Das Genom umfasst die Gesamtheit der genetischen, vererbbaren Information eines Organismus. Die Sequenzierung des gesamten Genoms ermöglicht die Untersuchung von Variationen (Single Nucleotide Polymorphisms (SNP) und Structural Variants) innerhalb einer Spezies (GAN et al., 2011; EDWARDS et al., 2013) und Unterschieden zwischen verschiedenen Spezies. Problematisch bei der Rekonstruktion der kompletten Genomsequenz sind die durch die Sequenziertechnik bedingten sehr kurzen Reads und das Auftreten repetitiver Sequenzen, die bei der Assemblierung nicht eindeutig zugeordnet werden können. Neben einer Reihe von inzwischen komplett sequenzierten Nutzpflanzen wie Oryza sativa (GOFF et al., 2002), Hordeum vulgare (THE INTERNATIONAL BARLEY GENOME SEQUENCING CONSORTIUM et al., 2012), Zea mays (WEI et al., 2009), Triticum aestivum (BRENCHLEY et al., 2012) und Glycine max (SCHMUTZ et al., 2010) gilt Brachypodium distachyon (THE INTERNATIONAL BRACHYPODIUM INITIATIVE, 2010) aufgrund seines kleinen Genoms inzwischen als geeigneter Modellorganismus für Gräser. Da bisher nur wenige Pflanzengenome komplett sequenziert sind, werden hierfür in erster Linie de-novo-assemblierungstools verwendet (SCHATZ et al., 2012). Metagenom Das Metagenom bildet die Gesamtheit der genomischen Information der Mikroorganismen einer bestimmten Lebensgemeinschaft (Biozönose) oder eines Biotops. Da die Herkunftsspezies der genomischen Sequenzen hierbei nicht bekannt sind, müssen durch den Vergleich mit bereits bekannten Sequenzen zunächst die in der Probe (meist Umweltprobe aus Wasser oder Boden) enthaltenen Spezies bestimmt werden. Danach kann dann ihr Einfluss auf und ihre Interaktion mit z. B. Nutzpflanzen genauer untersucht werden. Julius-Kühn-Archiv, 443,
4 26. Deutsche Arbeitsbesprechung über Fragen der Unkrautbiologie und -bekämpfung, März 2014 in Braunschweig Geeignete Programme hierfür sind MEGAN (HUSON et al., 2007), mothur (SCHLOSS et al., 2009) und CLOTU (KUMAR et al., 2011). Exom Das Exom besteht aus den potenziell für Proteine kodierenden Abschnitten (Exons) der Gene eines Genoms. Um das Exom sequenzieren zu können, müssen zunächst die Exons aus dem Genom selektiert werden (sequence capture). Dies setzt voraus, dass eine Referenz-Genomsequenz der zu untersuchenden Spezies bereits bekannt ist. Da das Exom bei höheren Organismen nur einen kleinen Teil des Genoms ausmacht, ist es sehr viel kostengünstiger, das Exom anstelle weiterer Genome dieser Spezies zu sequenzieren, um Variationen in den kodierenden Bereichen zu untersuchen (MASCHER et al., 2013). Transkriptom Das Transkriptom repräsentiert die Gesamtheit der zu einem bestimmten Zeitpunkt unter bestimmten Bedingungen in einem Gewebe exprimierten Gene (d.h. die von der DNA in mrna transkribierten Gene). Unter Genexpression versteht man dabei die Ausprägung des Genotyps zum Phänotyp eines Organismus oder eines Gewebes. Da die mrna nicht direkt sequenziert werden kann, muss sie zunächst in cdna (complementary DNA) mit Hilfe des Enzyms Reverse Transkriptase umgeschrieben werden und die cdna kann dann anschließend sequenziert werden. Diese Technik wird als RNA-Seq bezeichnet (WANG et al., 2009). Das Transkriptom liefert zusammen mit dem Genom und dem Exom Informationen darüber, welche Exons durch alternatives Spleißen (alternative splicing) eines Gens zu einem bestimmten Zeitpunkt in welche mrna transkribiert werden (USADEL und FERNIE, 2013). Neben den auf Homologiesuche basierenden weit verbreiteten Tools BLAST, PSI-BLAST (ALTSCHUL et al., 1997), BLAT (KENT, 2002) und InterProScan (QUEVILLON et al., 2005) werden zur Annotation der sequenzierten Transkripte zunehmend auch Ontologien mit einem standardisierten Wortschatz verwendet (LOHSE et al., 2012). Für einen Überblick über die Transkriptomanalyse siehe GÓNGORA-CASTILLO und BUELL (2013), geeignete Programme für die Assemblierung eines Transkriptoms sind Trinity (GRABHERR et al., 2011) und Oases (SCHULZ et al., 2012). Neben der qualitativen Information über die in einer Probe enthaltenen Transkripte hinaus lassen sich mit RNA-Seq auch quantitative Daten gewinnen, d.h. Genexpressionsdaten, für die bisher Microarray-Experimente durchgeführt wurden. Auch wenn inzwischen ein großes Repertoir an statistischen Methoden zur Auswertung von Microarray-Experimenten existiert, haben sie den Nachteil, dass nur bekannte Transkripte nachgewiesen und verschiedene Experimente nur sehr aufwändig miteinander verglichen werden können (WANG et al., 2009). Durch die Weiterentwicklung geeigneter Tools zur Auswertung von RNA-Seq-Experimenten werden Microarray-Experimente daher in diesem Bereich zunehmend verdrängt. Zum exakten qualitativen und quantitativen Nachweis genetischen Materials bzw. der Expression einzelner Gene ist die Quantitative Real-Time-PCR (qrt-pcr oder qpcr) geeignet. Hierbei werden während der Durchführung der PCR Fluoreszenzsignale der amplifizierten Sequenzen gemessen. Voraussetzung für einen quantitativen Nachweis ist das Vorhandensein eines Referenzgens, dessen Expression gleichzeitig gemessen wird und zur Normalisierung der Expression des Zielgens dient. Als Referenzgen wird üblicherweise ein housekeeping gene verwendet, dessen Expression unabhängig von äußeren Einflüssen in allen Zellen und Geweben konstant sein sollte. Da auch hier die Expression über das Vorhandensein von mrna gemessen wird, für die Durchführung der PCR jedoch DNA benötigt wird, muss die mrna zunächst mit Hilfe des Enzyms Reverse Transkriptase in cdna umgeschrieben werden. Das gesamte Verfahren wird dann als RT-PCR (reverse transcription PCR) bezeichnet (HOLZAPFEL und WICKERT, 2007; DUHOUX und DÉLYE, 2013). Metabolom Die Metabolomik umfasst alle charakteristischen Stoffwechsel-Eigenschaften einer Zelle, eines Gewebes oder eines Organismus und geht damit über die Analyse von Genom, Transkriptom und Proteom hinaus hin zum Verständnis des Gesamtsystems (Systembiologie) einschließlich der 20 Julius-Kühn-Archiv, 443, 2014
5 beteiligten Metaboliten (MACEL et al., 2010). Da bisher weder Hochdurchsatz-Technologien zur Charakterisierung und Quantifizierung von Metaboliten noch Referenzdatenbanken existieren, ist die Metabolomik das bisher am wenigsten fortgeschrittene omik -Fachgebiet (HEGEMAN, 2010; DÉLYE, 2013). Zukünftige Entwicklungen werden dann auch eine gemeinsame Betrachtung von Metagenom- und Metabolomdaten (environmental metabolomics) möglich machen (BRUNETTI et al., 2013). Zur Analyse von Veränderungen im Stoffwechsel von Pflanzen unter unterschiedlichen Bedingungen können jedoch bereits Expressions- und Transkriptomdaten z. B. mit dem Tool MAPMAN auf bekannte Stoffwechselwege projiziert werden (THIMM et al., 2004; USADEL et al., 2009). Epigenom Unter Epigenetik werden alle genetischen Faktoren zusammengefasst, die auf Veränderungen an den Chromosomen (z. B. DNA-Methylierung, Histon-Modifikation) beruhen, ohne dass eine Veränderung der DNA-Sequenz zugrunde liegt. Einzelne Abschnitte oder ganze Chromosomen können so in ihrer Aktivität beeinflusst werden. Diese Veränderungen können durch Umwelteinflüsse (z. B. große Trockenheit) verursacht sein und an die Folgegeneration vererbt werden (KINOSHITA und JACOBSEN, 2012). Neueste Entwicklungen (Bisulfit-Sequenzierung, BS-Seq) ermöglichen erste Einblicke in das Methylierungsmuster kompletter Genome (DINH et al., 2012). Ausblick Die Entwicklung neuer Sequenziertechniken ermöglicht die Bearbeitung völlig neuer Fragestellungen sowohl in der der Medizin als auch den Agrarwissenschaften. Dadurch sind jedoch auch die Anforderungen an leistungsfähige Soft- und Hardware stark gestiegen und die Menge an Daten ist der aktuellen Entwicklung von Methoden (SCHLIESKY et al., 2012) und gebrauchsfähiger Software weit voraus. Damit ist momentan nicht mehr die Erzeugung der Daten der einschränkende Faktor sondern ihre anschließende Speicherung, Verarbeitung, Analyse und Interpretation am Computer. Um die vielfältigen Möglichkeiten der verfügbaren computergestützten Methoden optimal nutzen zu können, ist auf der einen Seite eine Entwicklung zu benutzerfreundlicherer Software (GOFF et al., 2011; SMITH, 2013) und auf der anderen Seite die Bereitschaft von Medizinern, Biologen und Agrarwissenschaftlern nötig, diese Methoden als weitere Werkzeuge in ihren Arbeitsalltag zu integrieren (SERVICE, 2013). Literatur ALTSCHUL, S. F., T. L. MADDEN, A. A. SCHÄFFER, J. ZHANG, Z. ZHANG, W. MILLER und D. J. LIPMAN, 1997: Gapped BLAST and PSI-BLAST: a new generation of protein database search programs. Nucleic Acids Res. 25(17), BRENCHLEY, R., M. SPANNAGL, M. PFEIFER, G. L. BARKER, R. D'AMORE, A. M. ALLEN, N. MCKENZIE, M. KRAMER, A. KERHORNOU, D. BOLSER, S. KAY, D. WAITE, M. TRICK, I. BANCROFT, Y. GU, N. HUO, M.-C. LUO, S. SEHGAL, B. GILL, S. KIANIAN, O. ANDERSON, P. KERSEY, J. DVORAK, W. R. MCCOMBIE, A. HALL, K. F. X. MAYER, K. J. EDWARDS, M. W. BEVAN und N. HALL, 2012: Analysis of the bread wheat genome using whole-genome shotgun sequencing. Nature 491(7426), BRUNETTI, C., R. M. GEORGE, M. TATTINI, K. FIELD und M. P. DAVEY, 2013: Metabolomics in plant environmental physiology. J. Exp. Bot. 64(13), CAO, J., K. SCHNEEBERGER, S. OSSOWSKI, T. GÜNTHER, S. BENDER, J. FITZ, D. KOENIG, C. LANZ, O. STEGLE, C. LIPPERT, X. WANG, F. OTT, J. MÜLLER, C. ALONSO-BLANCO, K. BORGWARDT, K. J. SCHMID und D. WEIGEL, 2011: Whole-genome sequencing of multiple Arabidopsis thaliana populations. Nat. Genet. 43(10), DÉLYE, C., 2013: Unravelling the genetic bases of non-target-site-based resistance (NTSR) to herbicides: a major challenge for weed science in the forthcoming decade. Pest Manag. Sci. 69(2), DINH, H. Q., M. DUBIN, F. J. SEDLAZECK, N. LETTNER, O. MITTELSTEN SCHEID und A. VON HAESELER, 2012: Advanced methylome analysis after bisulfite deep sequencing: an example in Arabidopsis. PLoS One. 7(7), e DUHOUX, A., und C. DÉLYE, 2013: Reference genes to study herbicide stress response in Lolium sp.: up-regulation of P450 genes in plants resistant to acetolactate-synthase inhibitors. PLoS One. 8(5), e DUVICK, J., A. FU, U. MUPPIRALA, M. SABHARWAL, M. D. WILKERSON, C. J. LAWRENCE, C. LUSHBOUGH und V. BRENDEL, 2008: PlantGDB: a resource for comparative plant genomics. Nucleic Acids Res. 36(Database issue), D959-D965. EDWARDS, D., J. BATLEY, und R. J. SNOWDON, 2013: Accessing complex crop genomes with next-generation sequencing. Theor. Appl. Genet. 126(1), Julius-Kühn-Archiv, 443,
6 26. Deutsche Arbeitsbesprechung über Fragen der Unkrautbiologie und -bekämpfung, März 2014 in Braunschweig FLICEK, P., I. AHMED, M. R. AMODE, D. BARRELL, K. BEAL, S. BRENT, D. CARVALHO-SILVA, P. CLAPHAM, G. COATES, S. FAIRLEY, S. FITZGERALD, L. GIL, C. GARCÍA-GIRÓN, L. GORDON, T. HOURLIER, S. HUNT, T. JUETTEMANN, A. K. KÄHÄRI, S. KEENAN, M. KOMOROWSKA, E. KULESHA, I. LONGDEN, T. MAUREL, W. M. MCLAREN, M. MUFFATO, R. NAG, B. OVERDUIN, M. PIGNATELLI, B. PRITCHARD, E. PRITCHARD, H. S. RIAT, G. R. S. RITCHIE, M. RUFFIER, M. SCHUSTER, D. SHEPPARD, D. SOBRAL, K. TAYLOR, A. THORMANN, S. TREVANION, S. WHITE, S. P. WILDER, B. L. AKEN, E. BIRNEY, F. CUNNINGHAM, I. DUNHAM, J. HARROW, J. HERRERO, T. J. P. HUBBARD, N. JOHNSON, R. KINSELLA, A. PARKER, G. SPUDICH, A. YATES, A. ZADISSA und S. M. J. SEARLE, 2013: Ensembl Nucleic Acids Res. 41(Database issue), D48-D55. GAN, X., O. STEGLE, J. BEHR, J. G. STEFFEN, P. DREWE, K. L. HILDEBRAND, R. LYNGSOE, S. J. SCHULTHEISS, E. J. OSBORNE, V. T. SREEDHARAN, A. KAHLES, R. BOHNERT, G. JEAN, P. DERWENT, P. KERSEY, E. J. BELFIELD, N. P. HARBERD, E. KEMEN, C. TOOMAJIAN, P. X. KOVER, R. M. CLARK, G. RÄTSCH und R. MOTT, 2011: Multiple reference genomes and transcriptomes for Arabidopsis thaliana. Nature 477(7365), GOFF, S. A., M. VAUGHN, S. MCKAY, E. LYONS, A. E. STAPLETON, D. GESSLER, N. MATASCI, L. WANG, M. HANLON, A. LENARDS, A. MUIR, N. MERCHANT, S. LOWRY, S. MOCK, M. HELMKE, A. KUBACH, M. NARRO, N. HOPKINS, D. MICKLOS, U. HILGERT, M. GONZALES, C. JORDAN, E. SKIDMORE, R. DOOLEY, J. CAZES, R. MCLAY, Z. LU, S. PASTERNAK, L. KOESTERKE, W. H. PIEL, R. GRENE, C. NOUTSOS, K. GENDLER, X. FENG, C. TANG, M. LENT, S.-J. KIM, K. KVILEKVAL, B. S. MANJUNATH, V. TANNEN, A. STAMATAKIS, M. SANDERSON, S. M. WELCH, K. A. CRANSTON, P. SOLTIS, D. SOLTIS, B. O'MEARA, C. ANE, T. BRUTNELL, D. J. KLEIBENSTEIN, J. W. WHITE, J. LEEBENS-MACK, M. J. DONOGHUE, E. P. SPALDING, T. J. VISION, C. R. MYERS, D. LOWENTHAL, B. J. ENQUIST, B. BOYLE, A. AKOGLU, G. ANDREWS, S. RAM, D. WARE, L. STEIN und D. STANZIONE, 2011: The iplant Collaborative: Cyberinfrastructure for Plant Biology. Front. Plant Sci. 2, 34. GOFF, S. A., D. RICKE, T.-H. LAN, G. PRESTING, R. WANG, M. DUNN, J. GLAZEBROOK, A. SESSIONS, P. OELLER, H. VARMA, D. HADLEY, D. HUTCHISON, C. MARTIN, F. KATAGIRI, B. M. LANGE, T. MOUGHAMER, Y. XIA, P. BUDWORTH, J. ZHONG, T. MIGUEL, U. PASZKOWSKI, S. ZHANG, M. COLBERT, W.-I. SUN, L. CHEN, B. COOPER, S. PARK, T. C. WOOD, L. MAO, P. QUAIL, R. WING, R. DEAN, Y. YU, A. ZHARKIKH, R. SHEN, S. SAHASRABUDHE, A. THOMAS, R. CANNINGS, A. GUTIN, D. PRUSS, J. REID, S. TAVTIGIAN, J. MITCHELL, G. ELDREDGE, T. SCHOLL, R. M. MILLER, S. BHATNAGAR, N. ADEY, T. RUBANO, N. TUSNEEM, R. ROBINSON, J. FELDHAUS, T. MACALMA, A. OLIPHANT und S. BRIGGS, 2002: A draft sequence of the rice genome (Oryza sativa L. ssp. japonica). Science 296(5565), GÓNGORA-CASTILLO, E. und C. R. BUELL, 2013: Bioinformatics challenges in de novo transcriptome assembly using short read sequences in the absence of a reference genome sequence. Nat. Prod. Rep. 30(4), GOODSTEIN, D. M., S. SHU, R. HOWSON, R. NEUPANE, R. D. HAYES, J. FAZO, T. MITROS, W. DIRKS, U. HELLSTEN, N. PUTNAM und D. ROKHSAR, 2012: Phytozome: a comparative platform for green plant genomics. Nucleic Acids Res. 40(Database issue), D1178-D1186. GRABHERR, M. G., B. J. HAAS, M. YASSOUR, J. Z. LEVIN, D. A. THOMPSON, I. AMIT, X. ADICONIS, L. FAN, R. RAYCHOWDHURY, Q. ZENG, Z. CHEN, E. MAUCELI, N. HACOHEN, A. GNIRKE, N. RHIND, F. DI PALMA, B. W. BIRREN, C. NUSBAUM, K. LINDBLAD-TOH, N. FRIEDMAN und A. REGEV, 2011: Full-length transcriptome assembly from RNA-Seq data without a reference genome. Nat. Biotechnol. 29(7), HEGEMAN, A. D., 2010: Plant metabolomics - meeting the analytical challenges of comprehensive metabolite analysis. Brief. Funct. Genomics. 9(2), HOLZAPFEL, B. und L. WICKERT, 2007: Die quantitative Real-Time-PCR (qrt-pcr). Methoden und Anwendungsgebiete. Biol. Unserer Zeit. 37(2), HUSON, D. H., A. F. AUCH, J. QI und S. C. SCHUSTER, 2007: MEGAN analysis of metagenomic data. Genome Res. 17(3), KENT, W. J., 2002: BLAT - the BLAST-like alignment tool. Genome Res. 12(4), KINOSHITA, T. und S. E. JACOBSEN, 2012: Opening the door to epigenetics in PCP. Plant Cell Physiol. 53(5), KUMAR, S., T. CARLSEN, B.-H. MEVIK, P. ENGER, R. BLAALID, K. SHALCHIAN-TABRIZI und H. KAUSERUD, 2011: CLOTU: an online pipeline for processing and clustering of 454 amplicon reads into OTUs followed by taxonomic annotation. BMC Bioinformatics. 12, 182. LAMESCH, P., T. Z. BERARDINI, D. LI, D. SWARBRECK, C. WILKS, R. SASIDHARAN, R. MULLER, K. DREHER, D. L. ALEXANDER, M. GARCIA-HERNANDEZ, A. S. KARTHIKEYAN, C. H. LEE, W. D. NELSON, L. PLOETZ, S. SINGH, A. WENSEL und E. HUALA, 2012: The Arabidopsis Information Resource (TAIR): improved gene annotation and new tools. Nucleic Acids Res. 40(Database issue), D1202-D1210. LOHSE, M. und B. USADEL, 2012: Klassifikation pflanzlicher Genome im Schnelldurchlauf. BIOspektrum 18(3), LOHSE, M., A. M. BOLGER, A. NAGEL, A. R. FERNIE, J. E. LUNN, M. STITT und B. USADEL, 2012: RobiNA: a user-friendly, integrated software solution for RNA-Seq-based transcriptomics. Nucleic Acids Res. 40(Web Server issue), W622-W627. MACEL, M., N. M. VAN DAM und J. J. KEURENTJES, 2010: Metabolomics: the chemistry between ecology and genetics. Mol. Ecol. Resour. 10(4), MASCHER, M., T. A. RICHMOND, D. J. GERHARDT, A. HIMMELBACH, L. CLISSOLD, D. SAMPATH, S. AYLING, B. STEUERNAGEL, M. PFEIFER, M. D'ASCENZO, E. D. AKHUNOV, P. E. HEDLEY, A. M. GONZALES, P. L. MORRELL, B. KILIAN, F. R. BLATTNER, U. SCHOLZ, K. F. X. MAYER, A. J. FLAVELL, G. J. MUEHLBAUER, R. WAUGH, J. A. JEDDELOH und N. STEIN, 2013: Barley whole exome capture: a tool for genomic research in the genus Hordeum and beyond. Plant J. [Epub ahead of publication]. NAGARAJAN, N. und M. POP, 2013: Sequence assembly demystified. Nat. Rev. Genet. 14(3), NUSSBAUMER, T., M. M. MARTIS, S. K. ROESSNER, M. PFEIFER, K. C. BADER, S. SHARMA, H. GUNDLACH und M. SPANNAGL, 2013: MIPS PlantsDB: a database framework for comparative plant genome research. Nucleic Acids Res. 41(Database issue), D1144-D1151. QUEVILLON, E., V. SILVENTOINEN, S. PILLAI, N. HARTE, N., MULDER, R. APWEILER und R. LOPEZ, 2005: InterProScan: protein domains identifier. Nucleic Acids Res. 33(Web Server issue), W116-W120. SCHATZ, M. C., J. WITKOWSKI und W. R. MCCOMBIE, 2012: Current challenges in de novo plant genome sequencing and assembly. Genome Biol. 13(4), 243. SCHLIESKY, S., U. GOWIK, A. P. WEBER und A. BRÄUTIGAM, 2012: RNA-Seq Assembly - Are We There Yet? Front. Plant Sci. 3, Julius-Kühn-Archiv, 443, 2014
7 SCHLOSS, P. D., S. L. WESTCOTT, T. RYABIN, J. R. HALL, M. HARTMANN, E. B. HOLLISTER, R. A. LESNIEWSKI, B. B. OAKLEY, D. H. PARKS, C. J. ROBINSON, J. W. SAHL, B. STRES, G. G. THALLINGER, D. J. VAN HORN und C. F. WEBER, 2009: Introducing mothur: open-source, platform-independent, community-supported software for describing and comparing microbial communities. Appl. Environ. Microbiol. 75(23), SCHMUTZ, J., S. B. CANNON, J. SCHLUETER, J. MA, T. MITROS, W. NELSON, D. L. HYTEN, Q. SONG, J. J. THELEN, J. CHENG, D. XU, U. HELLSTEN, G. D. MAY, Y. YU, T. SAKURAI, T. UMEZAWA, M. K. BHATTACHARYYA, D. SANDHU, B. VALLIYODAN, E. LINDQUIST, M. PETO, D. GRANT, S. SHU, D. GOODSTEIN, K. BARRY, M. FUTRELL-GRIGGS, B. ABERNATHY, J. DU, Z. TIAN, L. ZHU, N. GILL, T. JOSHI, M. LIBAULT, A. SETHURAMAN, X.-C. ZHANG, K. SHINOZAKI, H. T. NGUYEN, R. A. WING, P. CREGAN, J. SPECHT, J. GRIMWOOD, D. ROKHSAR, G. STACEY, R. C. SHOEMAKER und S. A. JACKSON, 2010: Genome sequence of the palaeopolyploid soybean. Nature 463(7278), SCHULZ, M. H., D. R. ZERBINO, M. VINGRON und E. BIRNEY, 2012: Oases: robust de novo RNA-seq assembly across the dynamic range of expression levels. Bioinformatics 28(8), SERVICE, R. F., 2013: Biology's Dry Future. Science 342(6155), SMITH, D. R., 2013: The battle for user-friendly bioinformatics. Front. Genet. 4, 187. THE ARABIDOPSIS GENOME INITIATIVE, 2000: Analysis of the genome sequence of the flowering plant Arabidopsis thaliana. Nature 408(6814), THE INTERNATIONAL BARLEY GENOME SEQUENCING CONSORTIUM, K. F. MAYER, R. WAUGH, J. W. BROWN, A. SCHULMAN, P. LANGRIDGE, M. PLATZER, G. B. FINCHER, G. J. MUEHLBAUER, K. SATO, T. J. CLOSE, R. P. WISE und N. STEIN, 2012: A physical, genetic and functional sequence assembly of the barley genome. Nature 491(7426), THE INTERNATIONAL BRACHYPODIUM INITIATIVE, 2010: Genome sequencing and analysis of the model grass Brachypodium distachyon. Nature 463(7282), THIMM, O., O. BLÄSING, Y. GIBON, A. NAGEL, S. MEYER, P. KRÜGER, J. SELBIG, L. A. MÜLLER, S. Y. RHEE und M. STITT, 2004: MAPMAN: a userdriven tool to display genomics data sets onto diagrams of metabolic pathways and other biological processes. Plant J. 37(6), USADEL, B., F. POREE, A. NAGEL, M. LOHSE, A. CZEDIK-EYSENBERG und M. STITT, 2009: A guide to using MapMan to visualize and compare Omics data in plants: a case study in the crop species, Maize. Plant Cell Environ. 32(9), USADEL, B. und A. R. FERNIE, 2013: The plant transcriptome - from integrating observations to models. Front. Plant. Sci. 4, 48. WANG, Z., M. GERSTEIN und M. SNYDER, 2009: RNA-Seq: a revolutionary tool for transcriptomics. Nat. Rev. Genet. 10(1), WEI, F., J. ZHANG, S. ZHOU, R. HE, M. SCHAEFFER, K. COLLURA, D. KUDRNA, B. P. FAGA, M. WISSOTSKI, W. GOLSER, S. M. ROCK, T. A. GRAVES, R. S. FULTON, E. COE, P. S. SCHNABLE, D. C. SCHWARTZ, D. WARE, S. W. CLIFTON, R. K. WILSON und R. A. WING, 2009: The physical and genetic framework of the maize B73 genome. PLoS Genet. 5(11), e WETTERSTRAND, K. A., 2013: DNA Sequencing Costs: Data from the NHGRI Genome Sequencing Program (GSP) Available at: Accessed YOUENS-CLARK, K., E. BUCKLER, T. CASSTEVENS, C. CHEN, G. DECLERCK, P. DERWENT, P. DHARMAWARDHANA, P. JAISWAL, P. KERSEY, A. S. KARTHIKEYAN, J. LU, S. R. MCCOUCH, L. REN, W. SPOONER, J. C. STEIN, J. THOMASON, S. WEI und D. WARE, 2011: Gramene database in 2010: updates and extensions. Nucleic Acids Res. 39(Database issue), D1085-D1094. ZHANG, P., K. DREHER, A. KARTHIKEYAN, A. CHI, A. PUJAR, R. CASPI, P. KARP, V. KIRKUP, M. LATENDRESSE, C. LEE, L. A. MUELLER, R. MULLER und S. Y. RHEE, 2010: Creation of a genome-wide metabolic pathway database for Populus trichocarpa using a new approach for reconstruction and curation of metabolic pathways for plants. Plant Physiol. 153(4), Julius-Kühn-Archiv, 443,
Neue DNA Sequenzierungstechnologien im Überblick
 Neue DNA Sequenzierungstechnologien im Überblick Dr. Bernd Timmermann Next Generation Sequencing Core Facility Max Planck Institute for Molecular Genetics Berlin, Germany Max-Planck-Gesellschaft 80 Institute
Neue DNA Sequenzierungstechnologien im Überblick Dr. Bernd Timmermann Next Generation Sequencing Core Facility Max Planck Institute for Molecular Genetics Berlin, Germany Max-Planck-Gesellschaft 80 Institute
Sequenziertechnologien
 Sequenziertechnologien Folien teilweise von G. Thallinger übernommen 11 Entwicklung der Sequenziertechnologie First Generation 1977 Sanger Sequenzierung (GOLD Standard) Second Generation 2005 454 Sequencing
Sequenziertechnologien Folien teilweise von G. Thallinger übernommen 11 Entwicklung der Sequenziertechnologie First Generation 1977 Sanger Sequenzierung (GOLD Standard) Second Generation 2005 454 Sequencing
NEXT-GENERATION SEQUENCING. Von der Probenvorbereitung bis zur bioinformatischen Auswertung
 FRAUNHOFER-INSTITUT FÜR GRENZFLÄCHEN- UND BIOVERFAHRENSTECHNIK IGB NEXT-GENERATION SEQUENCING Von der Probenvorbereitung bis zur bioinformatischen Auswertung »Progress in science depends on new techniques,
FRAUNHOFER-INSTITUT FÜR GRENZFLÄCHEN- UND BIOVERFAHRENSTECHNIK IGB NEXT-GENERATION SEQUENCING Von der Probenvorbereitung bis zur bioinformatischen Auswertung »Progress in science depends on new techniques,
Einblicke in das menschliche Erbgut (Genom) am Computer
 Einblicke in das menschliche Erbgut (Genom) am Computer Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de Binger Nacht der Wissenschaft - 16.04.2010 Das menschliche Genom ist entschlüsselt
Einblicke in das menschliche Erbgut (Genom) am Computer Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de Binger Nacht der Wissenschaft - 16.04.2010 Das menschliche Genom ist entschlüsselt
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr
 Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
UNIVERSITÄTSKLINIKUM Schleswig-Holstein. Sequenzierung. Norbert Arnold. Dept. Gynecology and Obstetrics Oncology Laboratory
 Sequenzierung Norbert Arnold Neue Sequenziertechnologien (seit 2005) Next Generation Sequenzierung (NGS, Erste Generation) Unterschiedliche Plattformen mit unterschiedlichen Strategien Roche 454 (basierend
Sequenzierung Norbert Arnold Neue Sequenziertechnologien (seit 2005) Next Generation Sequenzierung (NGS, Erste Generation) Unterschiedliche Plattformen mit unterschiedlichen Strategien Roche 454 (basierend
Genomsequenzierung für Anfänger
 Genomsequenzierung für Anfänger Philipp Pagel 8. November 2005 1 DNA Sequenzierung Heute wird DNA üblicherweise mit der sogenannten Sanger (oder chain-terminationoder Didesoxy-) Methode sequenziert dessen
Genomsequenzierung für Anfänger Philipp Pagel 8. November 2005 1 DNA Sequenzierung Heute wird DNA üblicherweise mit der sogenannten Sanger (oder chain-terminationoder Didesoxy-) Methode sequenziert dessen
Bioinformatik: Hype oder Hoffnung?
 Bioinformatik: Hype oder Hoffnung? Florian Markowetz Max-Planck-Institut für Molekulare Genetik Computational Molecular Biology Berlin Career Nights AKG Bensheim, 28. Januar 2005 1 Florian Markowetz, Bioinformatik:
Bioinformatik: Hype oder Hoffnung? Florian Markowetz Max-Planck-Institut für Molekulare Genetik Computational Molecular Biology Berlin Career Nights AKG Bensheim, 28. Januar 2005 1 Florian Markowetz, Bioinformatik:
Center for Biotechnology, Bielefeld
 Andreas Albersmeier CeBiTec Bielefeld 3. Life Science Conference Analytik Jena Jena 14.05.2014 Center for Biotechnology, Bielefeld sketchup.google.com Genomik Transkriptomik Proteomics Metabolomics Genom
Andreas Albersmeier CeBiTec Bielefeld 3. Life Science Conference Analytik Jena Jena 14.05.2014 Center for Biotechnology, Bielefeld sketchup.google.com Genomik Transkriptomik Proteomics Metabolomics Genom
SMART Newsletter Education Solutions April 2015
 SMART Education Newsletter April 2015 SMART Newsletter Education Solutions April 2015 Herzlich Willkommen zur aktuellen Ausgabe des Westcon & SMART Newsletters jeden Monat stellen wir Ihnen die neuesten
SMART Education Newsletter April 2015 SMART Newsletter Education Solutions April 2015 Herzlich Willkommen zur aktuellen Ausgabe des Westcon & SMART Newsletters jeden Monat stellen wir Ihnen die neuesten
Prozessbewertung und -verbesserung nach ITIL im Kontext des betrieblichen Informationsmanagements. von Stephanie Wilke am 14.08.08
 Prozessbewertung und -verbesserung nach ITIL im Kontext des betrieblichen Informationsmanagements von Stephanie Wilke am 14.08.08 Überblick Einleitung Was ist ITIL? Gegenüberstellung der Prozesse Neuer
Prozessbewertung und -verbesserung nach ITIL im Kontext des betrieblichen Informationsmanagements von Stephanie Wilke am 14.08.08 Überblick Einleitung Was ist ITIL? Gegenüberstellung der Prozesse Neuer
IT-Governance und Social, Mobile und Cloud Computing: Ein Management Framework... Bachelorarbeit
 IT-Governance und Social, Mobile und Cloud Computing: Ein Management Framework... Bachelorarbeit zur Erlangung des akademischen Grades Bachelor of Science (B.Sc.) im Studiengang Wirtschaftswissenschaft
IT-Governance und Social, Mobile und Cloud Computing: Ein Management Framework... Bachelorarbeit zur Erlangung des akademischen Grades Bachelor of Science (B.Sc.) im Studiengang Wirtschaftswissenschaft
SALSAH eine virtuelle Forschungsumgebung für die Geisteswissenschaften
 SALSAH eine virtuelle Forschungsumgebung für die Geisteswissenschaften Zusammenfassung: Abstract: Einführung genuin digital Virtuelle Forschungsumgebungen für die Geisteswissenschaften in Bezug auf die
SALSAH eine virtuelle Forschungsumgebung für die Geisteswissenschaften Zusammenfassung: Abstract: Einführung genuin digital Virtuelle Forschungsumgebungen für die Geisteswissenschaften in Bezug auf die
Erbgutanalyse mit wachsendem Automatisierungsgrad
 Powered by Seiten-Adresse: https://www.gesundheitsindustriebw.de/de/fachbeitrag/aktuell/erbgutanalyse-mitwachsendem-automatisierungsgrad/ Erbgutanalyse mit wachsendem Automatisierungsgrad Mit einer eigens
Powered by Seiten-Adresse: https://www.gesundheitsindustriebw.de/de/fachbeitrag/aktuell/erbgutanalyse-mitwachsendem-automatisierungsgrad/ Erbgutanalyse mit wachsendem Automatisierungsgrad Mit einer eigens
Übungsblatt: Protein interaction networks. Ulf Leser and Samira Jaeger
 Übungsblatt: Protein interaction networks Ulf Leser and Samira Jaeger Aufgabe 1 Netzwerkzentralität (6P) In der Vorlesung haben Degree Centrality besprochen. Finde drei weitere etablierte Zentralitätsmaße
Übungsblatt: Protein interaction networks Ulf Leser and Samira Jaeger Aufgabe 1 Netzwerkzentralität (6P) In der Vorlesung haben Degree Centrality besprochen. Finde drei weitere etablierte Zentralitätsmaße
Transcriptomics: Analysis of Microarrays
 Transcriptomics: Analysis of Microarrays Dion Whitehead dion@uni-muenster.de Division of Bioinformatics, Westfälische Wilhelms Universität Münster Microarrays Vorlesungsüberblick : 1. Überblick von Microarray
Transcriptomics: Analysis of Microarrays Dion Whitehead dion@uni-muenster.de Division of Bioinformatics, Westfälische Wilhelms Universität Münster Microarrays Vorlesungsüberblick : 1. Überblick von Microarray
Das Projekt wird durchgeführt von den Bezirksregierungen in Nordrhein- Westfalen in ihrer Funktion als Fachstelle für die öffentlichen Bibliotheken
 1 Das Projekt wird durchgeführt von den Bezirksregierungen in Nordrhein- Westfalen in ihrer Funktion als Fachstelle für die öffentlichen Bibliotheken welche die öffentlichen Bibliotheken im Bundesland
1 Das Projekt wird durchgeführt von den Bezirksregierungen in Nordrhein- Westfalen in ihrer Funktion als Fachstelle für die öffentlichen Bibliotheken welche die öffentlichen Bibliotheken im Bundesland
1. Erklären Sie das Prinzip der Sanger Sequenzierung. Klären Sie dabei folgende Punkte: a) Welche besondere Art von Nukleotiden wird verwendet und
 10. Methoden 1. Erklären Sie das Prinzip der Sanger Sequenzierung. Klären Sie dabei folgende Punkte: a) Welche besondere Art von Nukleotiden wird verwendet und welche Funktion haben diese bei der Sequenzierungsreaktion?
10. Methoden 1. Erklären Sie das Prinzip der Sanger Sequenzierung. Klären Sie dabei folgende Punkte: a) Welche besondere Art von Nukleotiden wird verwendet und welche Funktion haben diese bei der Sequenzierungsreaktion?
2. ERSTELLEN VON APPS MIT DEM ADT PLUGIN VON ECLIPSE
 2. ERSTELLEN VON APPS MIT DEM ADT PLUGIN VON ECLIPSE 2.1 Die Einrichtung der Benutzeroberfläche Das Einrichten einer Android-Eclipse-Entwicklungsumgebung zur Android-Entwicklung ist grundsätzlich nicht
2. ERSTELLEN VON APPS MIT DEM ADT PLUGIN VON ECLIPSE 2.1 Die Einrichtung der Benutzeroberfläche Das Einrichten einer Android-Eclipse-Entwicklungsumgebung zur Android-Entwicklung ist grundsätzlich nicht
Speicher in der Cloud
 Speicher in der Cloud Kostenbremse, Sicherheitsrisiko oder Basis für die unternehmensweite Kollaboration? von Cornelius Höchel-Winter 2013 ComConsult Research GmbH, Aachen 3 SYNCHRONISATION TEUFELSZEUG
Speicher in der Cloud Kostenbremse, Sicherheitsrisiko oder Basis für die unternehmensweite Kollaboration? von Cornelius Höchel-Winter 2013 ComConsult Research GmbH, Aachen 3 SYNCHRONISATION TEUFELSZEUG
Aktuell 2014 als Startseite der PK-Website auf Firefox einstellen
 SG April 2014 Aktuell 2014 als Startseite der PK-Website auf Firefox einstellen Stand 21.04.2014 PK 2014-1/58 Seite 1 von 5 Seiten Von den Besuchern der PK-Website verwenden inzwischen 54 % die Browser
SG April 2014 Aktuell 2014 als Startseite der PK-Website auf Firefox einstellen Stand 21.04.2014 PK 2014-1/58 Seite 1 von 5 Seiten Von den Besuchern der PK-Website verwenden inzwischen 54 % die Browser
Wann ist eine Software in Medizinprodukte- Aufbereitungsabteilungen ein Medizinprodukt?
 DGSV-Kongress 2009 Wann ist eine Software in Medizinprodukte- Aufbereitungsabteilungen ein Medizinprodukt? Sybille Andrée Betriebswirtin für und Sozialmanagement (FH-SRH) Prokuristin HSD Händschke Software
DGSV-Kongress 2009 Wann ist eine Software in Medizinprodukte- Aufbereitungsabteilungen ein Medizinprodukt? Sybille Andrée Betriebswirtin für und Sozialmanagement (FH-SRH) Prokuristin HSD Händschke Software
Fachbericht zum Thema: Anforderungen an ein Datenbanksystem
 Fachbericht zum Thema: Anforderungen an ein Datenbanksystem von André Franken 1 Inhaltsverzeichnis 1 Inhaltsverzeichnis 1 2 Einführung 2 2.1 Gründe für den Einsatz von DB-Systemen 2 2.2 Definition: Datenbank
Fachbericht zum Thema: Anforderungen an ein Datenbanksystem von André Franken 1 Inhaltsverzeichnis 1 Inhaltsverzeichnis 1 2 Einführung 2 2.1 Gründe für den Einsatz von DB-Systemen 2 2.2 Definition: Datenbank
Der Begriff Cloud. Eine Spurensuche. Patric Hafner 29.06.2012. geops
 Der Begriff Cloud Eine Spurensuche Patric Hafner geops 29.06.2012 Motivation Der größte Hype der IT-Branche Hype heißt sowohl Rummel als auch Schwindel slashdot.org The cloud represents a foundational
Der Begriff Cloud Eine Spurensuche Patric Hafner geops 29.06.2012 Motivation Der größte Hype der IT-Branche Hype heißt sowohl Rummel als auch Schwindel slashdot.org The cloud represents a foundational
Internet online Update (Internet Explorer)
 Um Ihr Consoir Beta immer schnell und umkompliziert auf den aktuellsten Stand zu bringen, bieten wir allen Kunden ein Internet Update an. Öffnen Sie Ihren Internetexplorer und gehen auf unsere Internetseite:
Um Ihr Consoir Beta immer schnell und umkompliziert auf den aktuellsten Stand zu bringen, bieten wir allen Kunden ein Internet Update an. Öffnen Sie Ihren Internetexplorer und gehen auf unsere Internetseite:
Würfelt man dabei je genau 10 - mal eine 1, 2, 3, 4, 5 und 6, so beträgt die Anzahl. der verschiedenen Reihenfolgen, in denen man dies tun kann, 60!.
 040304 Übung 9a Analysis, Abschnitt 4, Folie 8 Die Wahrscheinlichkeit, dass bei n - maliger Durchführung eines Zufallexperiments ein Ereignis A ( mit Wahrscheinlichkeit p p ( A ) ) für eine beliebige Anzahl
040304 Übung 9a Analysis, Abschnitt 4, Folie 8 Die Wahrscheinlichkeit, dass bei n - maliger Durchführung eines Zufallexperiments ein Ereignis A ( mit Wahrscheinlichkeit p p ( A ) ) für eine beliebige Anzahl
Klonierung von S2P Rolle der M19-Zellen. POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel
 Klonierung von S2P Rolle der M19-Zellen POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel Inhalt 1. Was ist eine humane genomische DNA-Bank? 2. Unterschied zwischen cdna-bank und genomischer DNA-Bank?
Klonierung von S2P Rolle der M19-Zellen POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel Inhalt 1. Was ist eine humane genomische DNA-Bank? 2. Unterschied zwischen cdna-bank und genomischer DNA-Bank?
Grundideen der Gentechnik
 Grundideen der Gentechnik Die Gentechnik kombiniert Biotechnik und Züchtung. Wie in der Züchtung wird die Erbinformation eines Lebewesen verändert. Dabei nutzte man in den Anfängen der Gentechnik vor allem
Grundideen der Gentechnik Die Gentechnik kombiniert Biotechnik und Züchtung. Wie in der Züchtung wird die Erbinformation eines Lebewesen verändert. Dabei nutzte man in den Anfängen der Gentechnik vor allem
Handbuch ECDL 2003 Basic Modul 5: Datenbank Grundlagen von relationalen Datenbanken
 Handbuch ECDL 2003 Basic Modul 5: Datenbank Grundlagen von relationalen Datenbanken Dateiname: ecdl5_01_00_documentation_standard.doc Speicherdatum: 14.02.2005 ECDL 2003 Basic Modul 5 Datenbank - Grundlagen
Handbuch ECDL 2003 Basic Modul 5: Datenbank Grundlagen von relationalen Datenbanken Dateiname: ecdl5_01_00_documentation_standard.doc Speicherdatum: 14.02.2005 ECDL 2003 Basic Modul 5 Datenbank - Grundlagen
Lineargleichungssysteme: Additions-/ Subtraktionsverfahren
 Lineargleichungssysteme: Additions-/ Subtraktionsverfahren W. Kippels 22. Februar 2014 Inhaltsverzeichnis 1 Einleitung 2 2 Lineargleichungssysteme zweiten Grades 2 3 Lineargleichungssysteme höheren als
Lineargleichungssysteme: Additions-/ Subtraktionsverfahren W. Kippels 22. Februar 2014 Inhaltsverzeichnis 1 Einleitung 2 2 Lineargleichungssysteme zweiten Grades 2 3 Lineargleichungssysteme höheren als
Bioinformatische Suche nach pre-mirnas
 Bioinformatische Suche nach pre-mirnas Vorbereitung: Lesen Sie die Publikationen Meyers et al., 2008, Criteria for Annotation of Plant MicroRNAs und Thieme et al., 2011, SplamiR prediction of spliced mirnas
Bioinformatische Suche nach pre-mirnas Vorbereitung: Lesen Sie die Publikationen Meyers et al., 2008, Criteria for Annotation of Plant MicroRNAs und Thieme et al., 2011, SplamiR prediction of spliced mirnas
Big Data Projekte richtig managen!
 Big Data Projekte richtig managen! Stuttgart, Oktober 2014 Praktische Herausforderungen eines Big Data Projektes Definition: Was ist Big Data? Big data is a collection of data sets so large and comple
Big Data Projekte richtig managen! Stuttgart, Oktober 2014 Praktische Herausforderungen eines Big Data Projektes Definition: Was ist Big Data? Big data is a collection of data sets so large and comple
Eva Douma: Die Vorteile und Nachteile der Ökonomisierung in der Sozialen Arbeit
 Eva Douma: Die Vorteile und Nachteile der Ökonomisierung in der Sozialen Arbeit Frau Dr. Eva Douma ist Organisations-Beraterin in Frankfurt am Main Das ist eine Zusammen-Fassung des Vortrages: Busines
Eva Douma: Die Vorteile und Nachteile der Ökonomisierung in der Sozialen Arbeit Frau Dr. Eva Douma ist Organisations-Beraterin in Frankfurt am Main Das ist eine Zusammen-Fassung des Vortrages: Busines
Mobile Intranet in Unternehmen
 Mobile Intranet in Unternehmen Ergebnisse einer Umfrage unter Intranet Verantwortlichen aexea GmbH - communication. content. consulting Augustenstraße 15 70178 Stuttgart Tel: 0711 87035490 Mobile Intranet
Mobile Intranet in Unternehmen Ergebnisse einer Umfrage unter Intranet Verantwortlichen aexea GmbH - communication. content. consulting Augustenstraße 15 70178 Stuttgart Tel: 0711 87035490 Mobile Intranet
APP-GFP/Fluoreszenzmikroskop. Aufnahmen neuronaler Zellen, mit freund. Genehmigung von Prof. Stefan Kins, TU Kaiserslautern
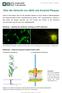 Über die Herkunft von Aβ42 und Amyloid-Plaques Heute ist sicher belegt, dass sich die amyloiden Plaques aus einer Vielzahl an Abbaufragmenten des Amyloid-Vorläufer-Proteins (amyloid-precursor-protein,
Über die Herkunft von Aβ42 und Amyloid-Plaques Heute ist sicher belegt, dass sich die amyloiden Plaques aus einer Vielzahl an Abbaufragmenten des Amyloid-Vorläufer-Proteins (amyloid-precursor-protein,
Web Interface für Anwender
 Ing. G. Michel Seite 1/5 Web Interface für Anwender 1) Grundlagen: - Sie benötigen die Zugangsdaten zu Ihrem Interface, welche Sie mit Einrichtung des Servers durch uns oder Ihren Administrator erhalten
Ing. G. Michel Seite 1/5 Web Interface für Anwender 1) Grundlagen: - Sie benötigen die Zugangsdaten zu Ihrem Interface, welche Sie mit Einrichtung des Servers durch uns oder Ihren Administrator erhalten
Unterrichtsmaterialien in digitaler und in gedruckter Form. Auszug aus: Übungsbuch für den Grundkurs mit Tipps und Lösungen: Analysis
 Unterrichtsmaterialien in digitaler und in gedruckter Form Auszug aus: Übungsbuch für den Grundkurs mit Tipps und Lösungen: Analysis Das komplette Material finden Sie hier: Download bei School-Scout.de
Unterrichtsmaterialien in digitaler und in gedruckter Form Auszug aus: Übungsbuch für den Grundkurs mit Tipps und Lösungen: Analysis Das komplette Material finden Sie hier: Download bei School-Scout.de
Labortechniken (2) Amplifikationskurve (linear linear) Realtime-PCR
 Realtime PCR Quantitative PCR Prinzip: Nachweis der PCR-Produkte in Echtzeit und Quantifizierung anhand eines fluoreszenten Reporters R Q Taq-Polymerase Synthese- und Nuklease-Einheit R=Reporter, Q=Quencher
Realtime PCR Quantitative PCR Prinzip: Nachweis der PCR-Produkte in Echtzeit und Quantifizierung anhand eines fluoreszenten Reporters R Q Taq-Polymerase Synthese- und Nuklease-Einheit R=Reporter, Q=Quencher
Windows Server 2012 R2 Essentials & Hyper-V
 erklärt: Windows Server 2012 R2 Essentials & Hyper-V Windows Server 2012 R2 Essentials bietet gegenüber der Vorgängerversion die Möglichkeit, mit den Boardmitteln den Windows Server 2012 R2 Essentials
erklärt: Windows Server 2012 R2 Essentials & Hyper-V Windows Server 2012 R2 Essentials bietet gegenüber der Vorgängerversion die Möglichkeit, mit den Boardmitteln den Windows Server 2012 R2 Essentials
SJ OFFICE - Update 3.0
 SJ OFFICE - Update 3.0 Das Update auf die vorherige Version 2.0 kostet netto Euro 75,00 für die erste Lizenz. Das Update für weitere Lizenzen kostet jeweils netto Euro 18,75 (25%). inkl. Programmsupport
SJ OFFICE - Update 3.0 Das Update auf die vorherige Version 2.0 kostet netto Euro 75,00 für die erste Lizenz. Das Update für weitere Lizenzen kostet jeweils netto Euro 18,75 (25%). inkl. Programmsupport
Folgende Voraussetzungen für die Konfiguration müssen erfüllt sein: - Ein Bootimage ab Version 7.4.4. - Optional einen DHCP Server.
 1. Dynamic Host Configuration Protocol 1.1 Einleitung Im Folgenden wird die Konfiguration von DHCP beschrieben. Sie setzen den Bintec Router entweder als DHCP Server, DHCP Client oder als DHCP Relay Agent
1. Dynamic Host Configuration Protocol 1.1 Einleitung Im Folgenden wird die Konfiguration von DHCP beschrieben. Sie setzen den Bintec Router entweder als DHCP Server, DHCP Client oder als DHCP Relay Agent
Genomische Selektion in der Pflanzenzüchtung
 Genomische Selektion in der Pflanzenzüchtung Chris-CarolinCarolin Schön 30. März 2012 Hybridzüchtung Population 1 Population 2 Kreuzungen 10.000000 Linieni Prüfung 1 Umwelt Kreuzungen 10.000000 Linen 2.000
Genomische Selektion in der Pflanzenzüchtung Chris-CarolinCarolin Schön 30. März 2012 Hybridzüchtung Population 1 Population 2 Kreuzungen 10.000000 Linieni Prüfung 1 Umwelt Kreuzungen 10.000000 Linen 2.000
Installation SQL- Server 2012 Single Node
 Installation SQL- Server 2012 Single Node Dies ist eine Installationsanleitung für den neuen SQL Server 2012. Es beschreibt eine Single Node Installation auf einem virtuellen Windows Server 2008 R2 mit
Installation SQL- Server 2012 Single Node Dies ist eine Installationsanleitung für den neuen SQL Server 2012. Es beschreibt eine Single Node Installation auf einem virtuellen Windows Server 2008 R2 mit
Agile Vorgehensmodelle in der Softwareentwicklung: Scrum
 C A R L V O N O S S I E T Z K Y Agile Vorgehensmodelle in der Softwareentwicklung: Scrum Johannes Diemke Vortrag im Rahmen der Projektgruppe Oldenburger Robot Soccer Team im Wintersemester 2009/2010 Was
C A R L V O N O S S I E T Z K Y Agile Vorgehensmodelle in der Softwareentwicklung: Scrum Johannes Diemke Vortrag im Rahmen der Projektgruppe Oldenburger Robot Soccer Team im Wintersemester 2009/2010 Was
Daten haben wir reichlich! 25.04.14 The unbelievable Machine Company 1
 Daten haben wir reichlich! 25.04.14 The unbelievable Machine Company 1 2.800.000.000.000.000.000.000 Bytes Daten im Jahr 2012* * Wenn jedes Byte einem Buchstaben entspricht und wir 1000 Buchstaben auf
Daten haben wir reichlich! 25.04.14 The unbelievable Machine Company 1 2.800.000.000.000.000.000.000 Bytes Daten im Jahr 2012* * Wenn jedes Byte einem Buchstaben entspricht und wir 1000 Buchstaben auf
Diese Ansicht erhalten Sie nach der erfolgreichen Anmeldung bei Wordpress.
 Anmeldung http://www.ihredomain.de/wp-admin Dashboard Diese Ansicht erhalten Sie nach der erfolgreichen Anmeldung bei Wordpress. Das Dashboard gibt Ihnen eine kurze Übersicht, z.b. Anzahl der Beiträge,
Anmeldung http://www.ihredomain.de/wp-admin Dashboard Diese Ansicht erhalten Sie nach der erfolgreichen Anmeldung bei Wordpress. Das Dashboard gibt Ihnen eine kurze Übersicht, z.b. Anzahl der Beiträge,
Q1 B1 KW 49. Genregulation
 Q1 B1 KW 49 Genregulation Transkription Posttranskription elle Modifikation Genregulation bei Eukaryoten Transkriptionsfaktoren (an TATA- Box) oder Silencer (verringert Transkription) und Enhancer (erhöht
Q1 B1 KW 49 Genregulation Transkription Posttranskription elle Modifikation Genregulation bei Eukaryoten Transkriptionsfaktoren (an TATA- Box) oder Silencer (verringert Transkription) und Enhancer (erhöht
Reporting Services und SharePoint 2010 Teil 1
 Reporting Services und SharePoint 2010 Teil 1 Abstract Bei der Verwendung der Reporting Services in Zusammenhang mit SharePoint 2010 stellt sich immer wieder die Frage bei der Installation: Wo und Wie?
Reporting Services und SharePoint 2010 Teil 1 Abstract Bei der Verwendung der Reporting Services in Zusammenhang mit SharePoint 2010 stellt sich immer wieder die Frage bei der Installation: Wo und Wie?
Leichte-Sprache-Bilder
 Leichte-Sprache-Bilder Reinhild Kassing Information - So geht es 1. Bilder gucken 2. anmelden für Probe-Bilder 3. Bilder bestellen 4. Rechnung bezahlen 5. Bilder runterladen 6. neue Bilder vorschlagen
Leichte-Sprache-Bilder Reinhild Kassing Information - So geht es 1. Bilder gucken 2. anmelden für Probe-Bilder 3. Bilder bestellen 4. Rechnung bezahlen 5. Bilder runterladen 6. neue Bilder vorschlagen
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2014
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2014 Fragen für die Übungsstunde 8 (14.07-18.07.) 1) Von der DNA-Sequenz zum Protein Sie können
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2014 Fragen für die Übungsstunde 8 (14.07-18.07.) 1) Von der DNA-Sequenz zum Protein Sie können
Psychologie im Arbeitsschutz
 Fachvortrag zur Arbeitsschutztagung 2014 zum Thema: Psychologie im Arbeitsschutz von Dipl. Ing. Mirco Pretzel 23. Januar 2014 Quelle: Dt. Kaltwalzmuseum Hagen-Hohenlimburg 1. Einleitung Was hat mit moderner
Fachvortrag zur Arbeitsschutztagung 2014 zum Thema: Psychologie im Arbeitsschutz von Dipl. Ing. Mirco Pretzel 23. Januar 2014 Quelle: Dt. Kaltwalzmuseum Hagen-Hohenlimburg 1. Einleitung Was hat mit moderner
Agentur für Werbung & Internet. Schritt für Schritt: E-Mail-Konfiguration mit Apple Mail
 Agentur für Werbung & Internet Schritt für Schritt: E-Mail-Konfiguration mit Apple Mail E-Mail-Konfiguration mit Apple Mail Inhalt E-Mail-Konto erstellen 3 Auswahl des Servertyp: POP oder IMAP 4 Konfiguration
Agentur für Werbung & Internet Schritt für Schritt: E-Mail-Konfiguration mit Apple Mail E-Mail-Konfiguration mit Apple Mail Inhalt E-Mail-Konto erstellen 3 Auswahl des Servertyp: POP oder IMAP 4 Konfiguration
Guide DynDNS und Portforwarding
 Guide DynDNS und Portforwarding Allgemein Um Geräte im lokalen Netzwerk von überall aus über das Internet erreichen zu können, kommt man um die Themen Dynamik DNS (kurz DynDNS) und Portweiterleitung(auch
Guide DynDNS und Portforwarding Allgemein Um Geräte im lokalen Netzwerk von überall aus über das Internet erreichen zu können, kommt man um die Themen Dynamik DNS (kurz DynDNS) und Portweiterleitung(auch
Ist Fernsehen schädlich für die eigene Meinung oder fördert es unabhängig zu denken?
 UErörterung zu dem Thema Ist Fernsehen schädlich für die eigene Meinung oder fördert es unabhängig zu denken? 2000 by christoph hoffmann Seite I Gliederung 1. In zu großen Mengen ist alles schädlich. 2.
UErörterung zu dem Thema Ist Fernsehen schädlich für die eigene Meinung oder fördert es unabhängig zu denken? 2000 by christoph hoffmann Seite I Gliederung 1. In zu großen Mengen ist alles schädlich. 2.
Lizenzen auschecken. Was ist zu tun?
 Use case Lizenzen auschecken Ihr Unternehmen hat eine Netzwerk-Commuterlizenz mit beispielsweise 4 Lizenzen. Am Freitag wollen Sie Ihren Laptop mit nach Hause nehmen, um dort am Wochenende weiter zu arbeiten.
Use case Lizenzen auschecken Ihr Unternehmen hat eine Netzwerk-Commuterlizenz mit beispielsweise 4 Lizenzen. Am Freitag wollen Sie Ihren Laptop mit nach Hause nehmen, um dort am Wochenende weiter zu arbeiten.
Step by Step Webserver unter Windows Server 2003. von Christian Bartl
 Step by Step Webserver unter Windows Server 2003 von Webserver unter Windows Server 2003 Um den WWW-Server-Dienst IIS (Internet Information Service) zu nutzen muss dieser zunächst installiert werden (wird
Step by Step Webserver unter Windows Server 2003 von Webserver unter Windows Server 2003 Um den WWW-Server-Dienst IIS (Internet Information Service) zu nutzen muss dieser zunächst installiert werden (wird
Moderne Behandlung des Grauen Stars
 Katarakt Moderne Behandlung des Grauen Stars Sehr geehrte Patientin, sehr geehrter Patient, Bei Ihnen wurde eine Trübung der Augenlinse festgestellt, die umgangssprachlich auch Grauer Star genannt wird.
Katarakt Moderne Behandlung des Grauen Stars Sehr geehrte Patientin, sehr geehrter Patient, Bei Ihnen wurde eine Trübung der Augenlinse festgestellt, die umgangssprachlich auch Grauer Star genannt wird.
Content Management System mit INTREXX 2002.
 Content Management System mit INTREXX 2002. Welche Vorteile hat ein CM-System mit INTREXX? Sie haben bereits INTREXX im Einsatz? Dann liegt es auf der Hand, dass Sie ein CM-System zur Pflege Ihrer Webseite,
Content Management System mit INTREXX 2002. Welche Vorteile hat ein CM-System mit INTREXX? Sie haben bereits INTREXX im Einsatz? Dann liegt es auf der Hand, dass Sie ein CM-System zur Pflege Ihrer Webseite,
Perspektive Großkonzern - Organisationen im Umbruch -
 - Organisationen im Umbruch - Universität Heidelberg Fakultät für Wirtschafts- und Sozialwissenschaften Max-Weber-Institut für Soziologie Seminar Entwicklungs- und Beratungsmethoden Seminarleitung: Dr.
- Organisationen im Umbruch - Universität Heidelberg Fakultät für Wirtschafts- und Sozialwissenschaften Max-Weber-Institut für Soziologie Seminar Entwicklungs- und Beratungsmethoden Seminarleitung: Dr.
Kurzanleitung OOVS. Reseller Interface. Allgemein
 Kurzanleitung OOVS Reseller Interface Allgemein Durch die Einführung des neuen Interfaces hat sich für Reseller von Syswebcom etwas geändert. Die Struktur der Kundenverwaltung ist einprägsamer, wenn man
Kurzanleitung OOVS Reseller Interface Allgemein Durch die Einführung des neuen Interfaces hat sich für Reseller von Syswebcom etwas geändert. Die Struktur der Kundenverwaltung ist einprägsamer, wenn man
GRUPPENPUZZLE: Hochdurchsatztechnologien in der Genomanalyse. Erste Lernphase: Aneignungsphase
 Folie GRUPPENPUZZLE: Hochdurchsatztechnologien in der Genomanalyse Erste Lernphase: Aneignungsphase Erarbeiten Sie in Ihrer Expertengruppe die Inhalte eines der vier Textabschnitte (2.1, 2.2, 3.1, 3.2).
Folie GRUPPENPUZZLE: Hochdurchsatztechnologien in der Genomanalyse Erste Lernphase: Aneignungsphase Erarbeiten Sie in Ihrer Expertengruppe die Inhalte eines der vier Textabschnitte (2.1, 2.2, 3.1, 3.2).
Whitepaper. Produkt: combit Relationship Manager 7. combit Relationship Manager email-rückläufer Script. combit GmbH Untere Laube 30 78462 Konstanz
 combit GmbH Untere Laube 30 78462 Konstanz Whitepaper Produkt: combit Relationship Manager 7 combit Relationship Manager email-rückläufer Script Inhalt Einleitung 3 Notwendige Anpassungen 3 crm Solution
combit GmbH Untere Laube 30 78462 Konstanz Whitepaper Produkt: combit Relationship Manager 7 combit Relationship Manager email-rückläufer Script Inhalt Einleitung 3 Notwendige Anpassungen 3 crm Solution
oqtans: Oqtans: Reproduzierbare, quantitative Transkriptom- Auswertung, auch in der Cloud Sebastian J. Schultheiss sjs@computomics.
 oqtans: Oqtans: Reproduzierbare, quantitative Transkriptom- Auswertung, auch in der Cloud Sebastian J. Schultheiss sjs@computomics.com Computomics GmbH & Co. KG und Friedrich Miescher Laboratory of the
oqtans: Oqtans: Reproduzierbare, quantitative Transkriptom- Auswertung, auch in der Cloud Sebastian J. Schultheiss sjs@computomics.com Computomics GmbH & Co. KG und Friedrich Miescher Laboratory of the
Ablaufbeschreibung für das neu Aufsetzen von Firebird und Interbase Datenbanken mit der IBOConsole
 Lavid-F.I.S. Ablaufbeschreibung für das neu Aufsetzen von Firebird und Interbase Datenbanken mit der Lavid Software GmbH Dauner Straße 12, D-41236 Mönchengladbach http://www.lavid-software.net Support:
Lavid-F.I.S. Ablaufbeschreibung für das neu Aufsetzen von Firebird und Interbase Datenbanken mit der Lavid Software GmbH Dauner Straße 12, D-41236 Mönchengladbach http://www.lavid-software.net Support:
Restore Exchange Server 2007 SP2
 1 Restore Exchange Server 2007 SP2 Diese Dokumentation beschreibt, wie Sie ein Restore Ihrer Exchange Datenbanken durchführen, wenn Sie das Backup mittels Windows Server Backup (WSB) erstellt haben. Das
1 Restore Exchange Server 2007 SP2 Diese Dokumentation beschreibt, wie Sie ein Restore Ihrer Exchange Datenbanken durchführen, wenn Sie das Backup mittels Windows Server Backup (WSB) erstellt haben. Das
Minimale Resterkrankung, Hochdurchsatz-Sequenzierung und Prognose beim multiplen Myelom
 Minimale Resterkrankung, Hochdurchsatz-Sequenzierung und Prognose beim multiplen Myelom Von Navneet Ramesh und Maike Haehle, übersetzt von Sabine Schock Vom 8. Apr 2014 7:41 Uhr; aktualisiert am 8. Apr
Minimale Resterkrankung, Hochdurchsatz-Sequenzierung und Prognose beim multiplen Myelom Von Navneet Ramesh und Maike Haehle, übersetzt von Sabine Schock Vom 8. Apr 2014 7:41 Uhr; aktualisiert am 8. Apr
40-Tage-Wunder- Kurs. Umarme, was Du nicht ändern kannst.
 40-Tage-Wunder- Kurs Umarme, was Du nicht ändern kannst. Das sagt Wikipedia: Als Wunder (griechisch thauma) gilt umgangssprachlich ein Ereignis, dessen Zustandekommen man sich nicht erklären kann, so dass
40-Tage-Wunder- Kurs Umarme, was Du nicht ändern kannst. Das sagt Wikipedia: Als Wunder (griechisch thauma) gilt umgangssprachlich ein Ereignis, dessen Zustandekommen man sich nicht erklären kann, so dass
Vermeiden Sie es sich bei einer deutlich erfahreneren Person "dranzuhängen", Sie sind persönlich verantwortlich für Ihren Lernerfolg.
 1 2 3 4 Vermeiden Sie es sich bei einer deutlich erfahreneren Person "dranzuhängen", Sie sind persönlich verantwortlich für Ihren Lernerfolg. Gerade beim Einstig in der Programmierung muss kontinuierlich
1 2 3 4 Vermeiden Sie es sich bei einer deutlich erfahreneren Person "dranzuhängen", Sie sind persönlich verantwortlich für Ihren Lernerfolg. Gerade beim Einstig in der Programmierung muss kontinuierlich
Use Cases. Use Cases
 Use Cases Eigenschaften: Ein Use Case beschreibt einen Teil des Verhaltens eines Systems aus externer Sicht (Formuliert in der der Fachsprache der Anwendung) Dies geschieht, indem ein Systemdialog beschrieben
Use Cases Eigenschaften: Ein Use Case beschreibt einen Teil des Verhaltens eines Systems aus externer Sicht (Formuliert in der der Fachsprache der Anwendung) Dies geschieht, indem ein Systemdialog beschrieben
Antibiotikaresistenz
 Unter versteht man die Eigenschaft von Mikroorganismen, die Wirkung antibiotisch aktiver Substanzen abschwächen oder gänzlich aufheben zu können. Grundsätzlich kann es in allen Bereichen, in denen Antibiotika
Unter versteht man die Eigenschaft von Mikroorganismen, die Wirkung antibiotisch aktiver Substanzen abschwächen oder gänzlich aufheben zu können. Grundsätzlich kann es in allen Bereichen, in denen Antibiotika
Wenn keine Verbindung zwischen den Computern besteht, dann bist du offline.
 online Das ist ein englisches Wort und bedeutet in der Leitung". Wenn du mit einem Freund oder einer Freundin telefonierst, bist du online. Wenn sich 2 Computer dein Computer und einer in Amerika miteinander
online Das ist ein englisches Wort und bedeutet in der Leitung". Wenn du mit einem Freund oder einer Freundin telefonierst, bist du online. Wenn sich 2 Computer dein Computer und einer in Amerika miteinander
THE KNOWLEDGE PEOPLE. CompanyFlyer.indd 1 07.03.2016 11:48:05
 THE KNOWLEDGE PEOPLE CompanyFlyer.indd 1 07.03.2016 11:48:05 BE SMART IT-CONSULTING Smartes IT-Consulting für die Zukunft: Agilität, Dynamische IT, Komplexitätsreduzierung, Cloud, Industrie 4.0, Big Data
THE KNOWLEDGE PEOPLE CompanyFlyer.indd 1 07.03.2016 11:48:05 BE SMART IT-CONSULTING Smartes IT-Consulting für die Zukunft: Agilität, Dynamische IT, Komplexitätsreduzierung, Cloud, Industrie 4.0, Big Data
Hauptprüfung Abiturprüfung 2015 (ohne CAS) Baden-Württemberg
 Hauptprüfung Abiturprüfung 205 (ohne CAS) Baden-Württemberg Wahlteil Analysis Hilfsmittel: GTR und Formelsammlung allgemeinbildende Gymnasien Alexander Schwarz www.mathe-aufgaben.com März 205 Aufgabe A
Hauptprüfung Abiturprüfung 205 (ohne CAS) Baden-Württemberg Wahlteil Analysis Hilfsmittel: GTR und Formelsammlung allgemeinbildende Gymnasien Alexander Schwarz www.mathe-aufgaben.com März 205 Aufgabe A
360 - Der Weg zum gläsernen Unternehmen mit QlikView am Beispiel Einkauf
 360 - Der Weg zum gläsernen Unternehmen mit QlikView am Beispiel Einkauf Von der Entstehung bis heute 1996 als EDV Beratung Saller gegründet, seit 2010 BI4U GmbH Firmensitz ist Unterschleißheim (bei München)
360 - Der Weg zum gläsernen Unternehmen mit QlikView am Beispiel Einkauf Von der Entstehung bis heute 1996 als EDV Beratung Saller gegründet, seit 2010 BI4U GmbH Firmensitz ist Unterschleißheim (bei München)
Also heißt es einmal mehr, immer eine eigene Meinungen bilden, nicht beeinflussen lassen, niemals von anderen irgend eine Meinung aufdrängen lassen.
 Seite 1 von 5 Wirtschaft, Finanzen und IT Computer und Technologie Internetseiten Übersichtlich alle verfügbaren Internetseiten von wirfinit. de und darüber hinaus, weitere empfehlenswerte Internetseiten
Seite 1 von 5 Wirtschaft, Finanzen und IT Computer und Technologie Internetseiten Übersichtlich alle verfügbaren Internetseiten von wirfinit. de und darüber hinaus, weitere empfehlenswerte Internetseiten
Merchant Center und Adwords Produkterweiterung mit Filter
 Letzte Aktualisierung: 02.02.2012 Merchant Center und Adwords Produkterweiterung mit Filter 1. In den USA kann man die Produkte selektieren (filtern), die zu einer Adwords- Anzeige als Produkterweiterung
Letzte Aktualisierung: 02.02.2012 Merchant Center und Adwords Produkterweiterung mit Filter 1. In den USA kann man die Produkte selektieren (filtern), die zu einer Adwords- Anzeige als Produkterweiterung
Homologie und Sequenzähnlichkeit. Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de
 Homologie und Sequenzähnlichkeit Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de Homologie Verwandtschaft aufgrund gleicher Abstammung basiert auf Speziation (Artbildung): aus einer
Homologie und Sequenzähnlichkeit Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de Homologie Verwandtschaft aufgrund gleicher Abstammung basiert auf Speziation (Artbildung): aus einer
Albert HAYR Linux, IT and Open Source Expert and Solution Architect. Open Source professionell einsetzen
 Open Source professionell einsetzen 1 Mein Background Ich bin überzeugt von Open Source. Ich verwende fast nur Open Source privat und beruflich. Ich arbeite seit mehr als 10 Jahren mit Linux und Open Source.
Open Source professionell einsetzen 1 Mein Background Ich bin überzeugt von Open Source. Ich verwende fast nur Open Source privat und beruflich. Ich arbeite seit mehr als 10 Jahren mit Linux und Open Source.
Ihr Mandant möchte einen neuen Gesellschafter aufnehmen. In welcher Höhe wäre eine Vergütung inklusive Tantieme steuerrechtlich zulässig?
 Ihr Mandant möchte einen neuen Gesellschafter aufnehmen. In welcher Höhe wäre eine Vergütung inklusive Tantieme steuerrechtlich zulässig? Oft wirft die Aufnahme neuer Gesellschafter oder auch die Einstellung
Ihr Mandant möchte einen neuen Gesellschafter aufnehmen. In welcher Höhe wäre eine Vergütung inklusive Tantieme steuerrechtlich zulässig? Oft wirft die Aufnahme neuer Gesellschafter oder auch die Einstellung
DNA Sequenzierung. Transkriptionsstart bestimmen PCR
 10. Methoden DNA Sequenzierung Transkriptionsstart bestimmen PCR 1. Erklären Sie das Prinzip der Sanger Sequenzierung. Klären Sie dabei folgende Punkte: a) Welche besondere Art von Nukleotiden wird verwendet
10. Methoden DNA Sequenzierung Transkriptionsstart bestimmen PCR 1. Erklären Sie das Prinzip der Sanger Sequenzierung. Klären Sie dabei folgende Punkte: a) Welche besondere Art von Nukleotiden wird verwendet
ALEXANDER NÉMETH A L E X A N D E R. N E M E T H @ I N T E R N A T I O N A L - P A R T N E R S. O R G + 4 9 ( 0 ) 1 5 1 1-2 5 7 1 1 5 6 24/09/2012
 1 ALEXANDER NÉMETH ANE PROJEKTMANAGEMENT UND TRAINING P R O U D M E M B E R OF T H E C L U B OF I N T E R N A T I O N A L P A R T N E R S Y O U R I N T E R N A T I O N A L T H I N K T A N K A L E X A N
1 ALEXANDER NÉMETH ANE PROJEKTMANAGEMENT UND TRAINING P R O U D M E M B E R OF T H E C L U B OF I N T E R N A T I O N A L P A R T N E R S Y O U R I N T E R N A T I O N A L T H I N K T A N K A L E X A N
Praktikum Nr. 3. Fachhochschule Bielefeld Fachbereich Elektrotechnik. Versuchsbericht für das elektronische Praktikum
 Fachhochschule Bielefeld Fachbereich Elektrotechnik Versuchsbericht für das elektronische Praktikum Praktikum Nr. 3 Manuel Schwarz Matrikelnr.: 207XXX Pascal Hahulla Matrikelnr.: 207XXX Thema: Transistorschaltungen
Fachhochschule Bielefeld Fachbereich Elektrotechnik Versuchsbericht für das elektronische Praktikum Praktikum Nr. 3 Manuel Schwarz Matrikelnr.: 207XXX Pascal Hahulla Matrikelnr.: 207XXX Thema: Transistorschaltungen
Die Lernumgebung des Projekts Informationskompetenz
 Beitrag für Bibliothek aktuell Die Lernumgebung des Projekts Informationskompetenz Von Sandra Merten Im Rahmen des Projekts Informationskompetenz wurde ein Musterkurs entwickelt, der den Lehrenden als
Beitrag für Bibliothek aktuell Die Lernumgebung des Projekts Informationskompetenz Von Sandra Merten Im Rahmen des Projekts Informationskompetenz wurde ein Musterkurs entwickelt, der den Lehrenden als
Barrierefreie Webseiten erstellen mit TYPO3
 Barrierefreie Webseiten erstellen mit TYPO3 Alternativtexte Für jedes Nicht-Text-Element ist ein äquivalenter Text bereitzustellen. Dies gilt insbesondere für Bilder. In der Liste der HTML 4-Attribute
Barrierefreie Webseiten erstellen mit TYPO3 Alternativtexte Für jedes Nicht-Text-Element ist ein äquivalenter Text bereitzustellen. Dies gilt insbesondere für Bilder. In der Liste der HTML 4-Attribute
Avira Management Console 2.6.1 Optimierung für großes Netzwerk. Kurzanleitung
 Avira Management Console 2.6.1 Optimierung für großes Netzwerk Kurzanleitung Inhaltsverzeichnis 1. Einleitung... 3 2. Aktivieren des Pull-Modus für den AMC Agent... 3 3. Ereignisse des AMC Agent festlegen...
Avira Management Console 2.6.1 Optimierung für großes Netzwerk Kurzanleitung Inhaltsverzeichnis 1. Einleitung... 3 2. Aktivieren des Pull-Modus für den AMC Agent... 3 3. Ereignisse des AMC Agent festlegen...
Stefan Rensing erforscht evolutionären Übergang von Algen zu Landpflanzen
 Powered by Seiten-Adresse: https://www.gesundheitsindustriebw.de/de/fachbeitrag/aktuell/stefan-rensing-erforschtevolutionaeren-bergang-von-algen-zu-landpflanzen/ Stefan Rensing erforscht evolutionären
Powered by Seiten-Adresse: https://www.gesundheitsindustriebw.de/de/fachbeitrag/aktuell/stefan-rensing-erforschtevolutionaeren-bergang-von-algen-zu-landpflanzen/ Stefan Rensing erforscht evolutionären
Anleitung auf SEITE 2
 Anleitung für den Zugang zum WLAN der UdK Berlin mit den SSIDs UdK Berlin (unsecure) unter Windows 7 Übersicht über die verschiedenen W-LANs an der UdK Berlin: W-LAN Vorteil Nachteil - Nutzerdaten werden
Anleitung für den Zugang zum WLAN der UdK Berlin mit den SSIDs UdK Berlin (unsecure) unter Windows 7 Übersicht über die verschiedenen W-LANs an der UdK Berlin: W-LAN Vorteil Nachteil - Nutzerdaten werden
How- to. E- Mail- Marketing How- to. Subdomain anlegen. Ihr Kontakt zur Inxmail Academy
 E- Mail- Marketing How- to How- to Subdomain anlegen Getrackte Links in Ihren E- Mails haben keinen Bezug zu Ihrer Domain und werden deswegen häufig von Ihren Empfängern als nicht vertrauenswürdig eingestuft.
E- Mail- Marketing How- to How- to Subdomain anlegen Getrackte Links in Ihren E- Mails haben keinen Bezug zu Ihrer Domain und werden deswegen häufig von Ihren Empfängern als nicht vertrauenswürdig eingestuft.
Einbindung einer ACT!12-16 Datenbank als Datenquelle für den Bulkmailer 2012
 Einbindung einer ACT!12-16 Datenbank als Datenquelle für den Bulkmailer 2012 Eine langvermisste Funktion ist mit den neuesten Versionen von ACT! und Bulkmailer wieder verfügbar. Mit dem Erscheinen der
Einbindung einer ACT!12-16 Datenbank als Datenquelle für den Bulkmailer 2012 Eine langvermisste Funktion ist mit den neuesten Versionen von ACT! und Bulkmailer wieder verfügbar. Mit dem Erscheinen der
Whitepaper. Produkt: address manager 2003. David XL Tobit InfoCenter AddIn für den address manager email Zuordnung
 combit GmbH Untere Laube 30 78462 Konstanz Whitepaper Produkt: address manager 2003 David XL Tobit InfoCenter AddIn für den address manager email Zuordnung David XL Tobit InfoCenter AddIn für den address
combit GmbH Untere Laube 30 78462 Konstanz Whitepaper Produkt: address manager 2003 David XL Tobit InfoCenter AddIn für den address manager email Zuordnung David XL Tobit InfoCenter AddIn für den address
Tipps & Tricks Neuerungen Nr. 5/ 2015. Externe Web-Shops im UniKat für Laborverbrauchsmaterial & Chemikalien
 Tipps & Tricks Neuerungen Nr. 5/ 2015 V01 08-06-2015 Externe Web-Shops im UniKat für Laborverbrauchsmaterial & Chemikalien Inhalt Einleitung... 2 Externe Web-Shops auswählen... 3 Artikelsuche und Artikelauswahl...
Tipps & Tricks Neuerungen Nr. 5/ 2015 V01 08-06-2015 Externe Web-Shops im UniKat für Laborverbrauchsmaterial & Chemikalien Inhalt Einleitung... 2 Externe Web-Shops auswählen... 3 Artikelsuche und Artikelauswahl...
Eigenen WSUS Server mit dem UNI WSUS Server Synchronisieren
 Verwaltungsdirektion Informatikdienste Eigenen WSUS Server mit dem UNI WSUS Server Synchronisieren Inhaltsverzeichnis Einleitung... 3 Installation WSUS Server... 4 Dokumente... 4 Step by Step Installation...
Verwaltungsdirektion Informatikdienste Eigenen WSUS Server mit dem UNI WSUS Server Synchronisieren Inhaltsverzeichnis Einleitung... 3 Installation WSUS Server... 4 Dokumente... 4 Step by Step Installation...
PK-Website: Besuche & Seitenaufrufe 2010 und 2011
 Abb. 2011-4/278 (Ausschnitt) PK-Website: Besuche & Seitenaufrufe bis 31. Dezember 2011, 248.993 Besuche, 425.183 Seitenaufrufe SG Dezember 2011 / Januar 2012 PK-Website: Besuche & Seitenaufrufe 2010 und
Abb. 2011-4/278 (Ausschnitt) PK-Website: Besuche & Seitenaufrufe bis 31. Dezember 2011, 248.993 Besuche, 425.183 Seitenaufrufe SG Dezember 2011 / Januar 2012 PK-Website: Besuche & Seitenaufrufe 2010 und
L10N-Manager 3. Netzwerktreffen der Hochschulübersetzer/i nnen Mannheim 10. Mai 2016
 L10N-Manager 3. Netzwerktreffen der Hochschulübersetzer/i nnen Mannheim 10. Mai 2016 Referentin: Dr. Kelly Neudorfer Universität Hohenheim Was wir jetzt besprechen werden ist eine Frage, mit denen viele
L10N-Manager 3. Netzwerktreffen der Hochschulübersetzer/i nnen Mannheim 10. Mai 2016 Referentin: Dr. Kelly Neudorfer Universität Hohenheim Was wir jetzt besprechen werden ist eine Frage, mit denen viele
Was ist PDF? Portable Document Format, von Adobe Systems entwickelt Multiplattformfähigkeit,
 Was ist PDF? Portable Document Format, von Adobe Systems entwickelt Multiplattformfähigkeit, Wie kann ein PDF File angezeigt werden? kann mit Acrobat-Viewern angezeigt werden auf jeder Plattform!! (Unix,
Was ist PDF? Portable Document Format, von Adobe Systems entwickelt Multiplattformfähigkeit, Wie kann ein PDF File angezeigt werden? kann mit Acrobat-Viewern angezeigt werden auf jeder Plattform!! (Unix,
Daten sammeln, darstellen, auswerten
 Vertiefen 1 Daten sammeln, darstellen, auswerten zu Aufgabe 1 Schulbuch, Seite 22 1 Haustiere zählen In der Tabelle rechts stehen die Haustiere der Kinder aus der Klasse 5b. a) Wie oft wurden die Haustiere
Vertiefen 1 Daten sammeln, darstellen, auswerten zu Aufgabe 1 Schulbuch, Seite 22 1 Haustiere zählen In der Tabelle rechts stehen die Haustiere der Kinder aus der Klasse 5b. a) Wie oft wurden die Haustiere
Schnittstelle DIGI-Zeiterfassung
 P.A.P.A. die kaufmännische Softwarelösung Schnittstelle DIGI-Zeiterfassung Inhalt Einleitung... 2 Eingeben der Daten... 2 Datenabgleich... 3 Zusammenfassung... 5 Es gelten ausschließlich unsere Allgemeinen
P.A.P.A. die kaufmännische Softwarelösung Schnittstelle DIGI-Zeiterfassung Inhalt Einleitung... 2 Eingeben der Daten... 2 Datenabgleich... 3 Zusammenfassung... 5 Es gelten ausschließlich unsere Allgemeinen
mysql - Clients MySQL - Abfragen eine serverbasierenden Datenbank
 mysql - Clients MySQL - Abfragen eine serverbasierenden Datenbank In den ersten beiden Abschnitten (rbanken1.pdf und rbanken2.pdf) haben wir uns mit am Ende mysql beschäftigt und kennengelernt, wie man
mysql - Clients MySQL - Abfragen eine serverbasierenden Datenbank In den ersten beiden Abschnitten (rbanken1.pdf und rbanken2.pdf) haben wir uns mit am Ende mysql beschäftigt und kennengelernt, wie man
Konzentration auf das. Wesentliche.
 Konzentration auf das Wesentliche. Machen Sie Ihre Kanzleiarbeit effizienter. 2 Sehr geehrte Leserin, sehr geehrter Leser, die Grundlagen Ihres Erfolges als Rechtsanwalt sind Ihre Expertise und Ihre Mandantenorientierung.
Konzentration auf das Wesentliche. Machen Sie Ihre Kanzleiarbeit effizienter. 2 Sehr geehrte Leserin, sehr geehrter Leser, die Grundlagen Ihres Erfolges als Rechtsanwalt sind Ihre Expertise und Ihre Mandantenorientierung.
