Algorithmen und Anwendungen zur Kartierung von Genomen
|
|
|
- Emil Adenauer
- vor 5 Jahren
- Abrufe
Transkript
1 Algorithmen und Anwendungen zur Kartierung von Genomen Dr. Dominik Grimm Probelehrveranstaltung Wissenschaftszentrum Straubing Hochschule Weihenstephan-Triesdorf Straubing, 14. Juli Juli 2017 Kartierung von Genomen 1
2 Inhalte & Lernziele dieser Vorlesung Was versteht man unter einer Kartierung des Genoms? Welche Arten von Kartierungen gibt es? Methoden zur Erstellung von physikalischen Karten Anwendung zur Kartierung von Genomen Zusammenfassung des Vorlesungsinhalts und Ausblick 14. Juli 2017 Kartierung von Genomen 2
3 Was versteht man unter einer Kartierung des Genoms? Motivation Finde den Weg von Haus A zu Haus B 14. Juli 2017 Kartierung von Genomen 3
4 Was versteht man unter einer Kartierung des Genoms? Motivation Füge Orientierungspunkte zur Karte hinzu 14. Juli 2017 Kartierung von Genomen 4
5 Was versteht man unter einer Kartierung des Genoms? Motivation Füge Orientierungspunkte zur Karte hinzu 14. Juli 2017 Kartierung von Genomen 5
6 Was versteht man unter einer Kartierung des Genoms? Motivation Hm ca. 50min ca. 20min ca. 40min 2 km 3 km 1.5 km Karten werden mit der Zeit und neueren Kartierungsmethoden immer detaillierter 14. Juli 2017 Kartierung von Genomen 6
7 Was versteht man unter einer Kartierung des Genoms? Arten der Genomkartierung Genetische Karte cm 14. Juli 2017 Kartierung von Genomen 7
8 Was versteht man unter einer Kartierung des Genoms? Arten der Genomkartierung Genetische Karte cm Zytogentische Karte 14. Juli 2017 Kartierung von Genomen 8
9 Was versteht man unter einer Kartierung des Genoms? Arten der Genomkartierung Genetische Karte cm Zytogentische Karte Physikalische Karte kb 14. Juli 2017 Kartierung von Genomen 9
10 Was versteht man unter einer Kartierung des Genoms? Arten der Genomkartierung Genetische Karte cm Zytogentische Karte Physikalische Karte kb DNA-Sequenz...ATGCCCCAGTAAGAGAGCATATATACAA... Basen 14. Juli 2017 Kartierung von Genomen 10
11 Was versteht man unter einer Kartierung des Genoms? Arten der Genomkartierung Genetische Karte cm Zytogentische Karte Physikalische Karte kb DNA-Sequenz...ATGCCCCAGTAAGAGAGCATATATACAA... Basen 14. Juli 2017 Kartierung von Genomen 11
12 Erstellung physikalischer Karten Restriktionsstellen-Kartierung Verfahren beruht auf Restriktionsenzymen à Sind in der Lage DNA-Motive zu erkennen und die DNA an diesen Stellen zu schneiden. EcoRI 5' 3' G A A T T C C T T A A G EcoRI 3' 5' 5' G A A T T C 3' 3' C T T A A G 5' 14. Juli 2017 Kartierung von Genomen 12
13 Erstellung physikalischer Karten Restriktionsstellen-Kartierung Restriktionsenzym schneidet DNA in Stücke unterschiedlicher Länge EcoRI Schnittstelle EcoRI Schnittstelle EcoRI 5Mb 0.5 Mb 3 Mb 1.5 Mb 14. Juli 2017 Kartierung von Genomen 13
14 Erstellung physikalischer Karten Restriktionsstellen-Kartierung Restriktionsenzym schneidet DNA in Stücke unterschiedlicher Länge EcoRI Schnittstelle EcoRI Schnittstelle 5Mb Marker EcoRI Marker 0.5 Mb 3 Mb 1.5 Mb Restriktionsschnittstellen sind spezifisch für jedes Restriktionsenzym 14. Juli 2017 Kartierung von Genomen 14
15 Erstellung physikalischer Karten Restriktionsstellen-Kartierung EcoRI Fragmente 20, 100, 200, Juli 2017 Kartierung von Genomen 15
16 Erstellung physikalischer Karten Restriktionsstellen-Kartierung EcoRI Fragmente 20, 100, 200, Juli 2017 Kartierung von Genomen 16
17 Erstellung physikalischer Karten Restriktionsstellen-Kartierung EcoRI Fragmente 20, 100, 200, Juli 2017 Kartierung von Genomen 17
18 Erstellung physikalischer Karten Restriktionsstellen-Kartierung Es gibt 4! = 24 mögliche Anordnungen (Permutationen) 14. Juli 2017 Kartierung von Genomen 18
19 Erstellung physikalischer Karten Restriktionsstellen-Kartierung Es gibt 4! = 24 mögliche Anordnungen (Permutationen) Wie kann man anhand der Fragmente die Reihenfolge der Marker (Restriktionsschnittstellen) rekonstruieren? 14. Juli 2017 Kartierung von Genomen 19
20 Erstellung physikalischer Karten Restriktionsstellen-Kartierung durch Double Digest DNA Restriktionsenzym A Restriktionsenzym B Restriktionsenzym A+B Längenmessung Fragmente A Längenmessung Fragmente B Längenmessung Fragmente A+B 14. Juli 2017 Kartierung von Genomen 20
21 Erstellung physikalischer Karten Restriktionsstellen-Kartierung durch Double Digest Längenmessung Fragmente A 20, 100, 200, 400 Längenmessung Fragmente B 50, 150, 220, 250 Längenmessung Fragmente A + B 20, 30, 50, 50, 80, 150, 170, Juli 2017 Kartierung von Genomen 21
22 Erstellung physikalischer Karten Restriktionsstellen-Kartierung durch Double Digest Enzym A Enzym B Juli 2017 Kartierung von Genomen 22
23 Erstellung physikalischer Karten Restriktionsstellen-Kartierung durch Double Digest Enzym A Enzym B Schnittmenge A+B Juli 2017 Kartierung von Genomen 23
24 Erstellung physikalischer Karten Restriktionsstellen-Kartierung durch Double Digest Enzym A Enzym B Schnittmenge A+B Juli 2017 Kartierung von Genomen 24
25 Erstellung physikalischer Karten Restriktionsstellen-Kartierung durch Double Digest Schnittmenge A+B Vergleiche Distanzen der Schnittmenge mit Längen der Fragmente A +B Längenmessung Fragmente A + B 20, 30, 50, 50, 80, 150, 170, Juli 2017 Kartierung von Genomen 25
26 Erstellung physikalischer Karten Restriktionsstellen-Kartierung durch Double Digest Schnittmenge A+B Vergleiche Distanzen der Schnittmenge mit Längen der Fragmente A +B Längenmessung Fragmente A + B 20, 30, 50, 50, 80, 150, 170, , 30, 50, 70, 80, 100, 120, , 30, 50, 50, 80, 150, 170, Juli 2017 Kartierung von Genomen 26
27 Erstellung physikalischer Karten Restriktionsstellen-Kartierung durch Double Digest Teste alle möglichen Kombinationen der Permutationen von A und B bis die Schnittmenge gleich der Fragmentlängenmessung von A + B ist. (in unserem Beispiel: 4!*4! = 576 Tests) 14. Juli 2017 Kartierung von Genomen 27
28 Erstellung physikalischer Karten Zusammenfassung Restriktionsstellen-Kartierung Double Digest ist experimentell leicht durchführbar Laufzeit ist exponentiell Es gibt nicht nur eine eindeutige Lösung (mehrere Lösungen möglich) 14. Juli 2017 Kartierung von Genomen 28
29 Erstellung physikalischer Karten Zusammenfassung Restriktionsstellen-Kartierung Double Digest ist experimentell leicht durchführbar Laufzeit ist exponentiell Es gibt nicht nur eine eindeutige Lösung (mehrere Lösungen möglich) à Effizientere Lösung mittels Partial Digest (nicht Teil dieser Vorlesung) jedoch auf Kosten des experimentellen Designs à Beide Methoden funktionieren nicht für große DNA-Strings à Fehler in der Verdauung oder Längenmessung werden nicht betrachtet 14. Juli 2017 Kartierung von Genomen 29
30 Für was werden physikalische Karten benötigt? Rekonstruktion von DNA-Sequenzen Wetterstrand KA. DNA Sequencing Costs: Data from the NHGRI Genome Sequencing Program (GSP) Available at: Accessed July Juli 2017 Kartierung von Genomen 30
31 Für was werden physikalische Karten benötigt? Rekonstruktion von DNA-Sequenzen DNA Kopien Fragmentierung ATGCATGCACGACAAGT AAGTAGGTTCCAAATTTTAAATGCC Sequenzierung AAATGCCCAGATAGAGAGAGAGA AGAGAGGGTTTTTACAGATAAGAGAGAG 14. Juli 2017 Kartierung von Genomen 31
32 Für was werden physikalische Karten benötigt? Rekonstruktion von DNA-Sequenzen Finden überlappender Sequenzen ATGCATGCACGACAAGT AAGTAGGTTCCAAATTTTAAATGCC AAAAGGGAGATAGAGAGAGAGA AGAGAGGGTTTTTACAGATAAGAGAGAG 14. Juli 2017 Kartierung von Genomen 32
33 Für was werden physikalische Karten benötigt? Rekonstruktion von DNA-Sequenzen Contig 1 Contig Juli 2017 Kartierung von Genomen 33
34 Für was werden physikalische Karten benötigt? Rekonstruktion von DNA-Sequenzen Contig 1 Contig 2 Physikalische Karten können dabei helfen die Contigs richtig anzuordnen 14. Juli 2017 Kartierung von Genomen 34
35 Anwendungen zur Kartierung des Genoms Anwendungen zur Kartierung des Genoms Genetische Karte cm Zytogentische Karte Physikalische Karte kb DNA-Sequenz...ATGCCCCAGTAAGAGAGCATATATACAA... Basen 14. Juli 2017 Kartierung von Genomen 35
36 Anwendungen zur Kartierung des Genoms Genomweite Assoziationsstudien (GWAS) Biomasse von Pflanzen Komplexe Krankheiten Metabolom eines Organismus Eigenschaften von Bakterien 14. Juli 2017 Kartierung von Genomen 36
37 Anwendungen zur Kartierung des Genoms Genomweite Assoziationsstudien (GWAS) Plant 1 Plant 2 Plant 3 Plant 4 Plant 5 Finde Assoziation zwischen Markern und Phänotyp 14. Juli 2017 Kartierung von Genomen 37
38 Anwendungen zur Kartierung des Genoms Human GWAS Catalog (Juni, 2017) Brustkrebs SNP-Trait Assoziationen Schizophrenie Alkoholabhängigkeit Typ-2 Diabetes Parkinson 14. Juli 2017 Kartierung von Genomen 38
39 Ausblick auf die nächste Vorlesung Was kommt als Nächstes? Restriktionsstellen-Kartierung durch Partial Digest Erläuterung der Partial Digest Methode Implementierung des Algorithmus in Python Kartierung durch Hybridisierung Unterschiedliche Algorithmen zur Erstellung physikalischer Karten durch Hybridisierungsexperimente Implementierung der Algorithmen in Python 14. Juli 2017 Kartierung von Genomen 39
40 Danksagung Berufungsausschuss Folien und Code zur Vorlesung Icons made by Freepik from is licensed under CC BY 3.0 Allen Zuhörern und Zuhörerinnen Zusätzliche Referenzen Brown, Terence A. "Mapping genomes." (2002). Böckenhauer, H. J., & Bongartz, D. (2003). Algorithmische Grundlagen der Bioinformatik: Modelle, Methoden und Komplexität. Springer-Verlag. Welter, D., MacArthur, J., Morales, J., Burdett, T., Hall, P., Junkins, H.,... & Parkinson, H. (2013). The NHGRI GWAS Catalog, a curated resource of SNP-trait associations. Nucleic acids research, 42(D1), D1001-D Juli 2017 Kartierung von Genomen 40
Ridge Regression und Kernalized Support Vector Machines : Einführung und Vergleich an einem Anwendungsbeispiel
 Ridge Regression und Kernalized Support Vector Machines : Einführung und Vergleich an einem Anwendungsbeispiel Dr. Dominik Grimm Probelehrveranstaltung Fakultät für Informatik und Mathematik Hochschule
Ridge Regression und Kernalized Support Vector Machines : Einführung und Vergleich an einem Anwendungsbeispiel Dr. Dominik Grimm Probelehrveranstaltung Fakultät für Informatik und Mathematik Hochschule
Bioinformatik Für Biophysiker
 Bioinformatik Für Biophysiker Sommersemester 2009 Silke Trißl / Ulf Leser Wissensmanagement in der Bioinformatik Wissensmanagement in der Bioinformatik Schwerpunkte Algorithmen der Bioinformatik Management
Bioinformatik Für Biophysiker Sommersemester 2009 Silke Trißl / Ulf Leser Wissensmanagement in der Bioinformatik Wissensmanagement in der Bioinformatik Schwerpunkte Algorithmen der Bioinformatik Management
Von Mendel bis -Omics Geschichte und Grundlagen der Humangenetik , Walther Vogel, Institut für Humangenetik
 Von Mendel bis -Omics Geschichte und Grundlagen der Humangenetik 19.04.2018, Walther Vogel, Institut für Humangenetik Erste Grundlagen ca 1850 bis 1900 Gregor Mendel (1822 1884) Erbfaktoren (Gene) dominant
Von Mendel bis -Omics Geschichte und Grundlagen der Humangenetik 19.04.2018, Walther Vogel, Institut für Humangenetik Erste Grundlagen ca 1850 bis 1900 Gregor Mendel (1822 1884) Erbfaktoren (Gene) dominant
Bioinformatik Für Biophysiker
 Bioinformatik Für Biophysiker Wintersemester 2005 / 2006 Ulf Leser Wissensmanagement in der Bioinformatik Wissensmanagement in der Bioinformatik Lehrstuhl seit 10/2002 Schwerpunkte Algorithmen der Bioinformatik
Bioinformatik Für Biophysiker Wintersemester 2005 / 2006 Ulf Leser Wissensmanagement in der Bioinformatik Wissensmanagement in der Bioinformatik Lehrstuhl seit 10/2002 Schwerpunkte Algorithmen der Bioinformatik
Übungen zu Algorithmische Bioinformatik
 Übungen zu Algorithmische Bioinformatik Philippe Thomas Samira Jaeger: Introduction to Bioinformatics, Exercises 1 1.) Sequenzen lesen (5Punkte) Für die Aufgabe müssen Sie Dateien einlesen, die DNA Sequenzen
Übungen zu Algorithmische Bioinformatik Philippe Thomas Samira Jaeger: Introduction to Bioinformatics, Exercises 1 1.) Sequenzen lesen (5Punkte) Für die Aufgabe müssen Sie Dateien einlesen, die DNA Sequenzen
Personalisierte Medizin
 Personalisierte Medizin Einblicke in das menschliche Genom aus Sicht der Bioinformatik Prof. Dr. Antje Krause FH Bingen a.krause@fh-bingen.de Kurzer Ausflug in die Genetik DNA (Desoxyribonukleinsäure)
Personalisierte Medizin Einblicke in das menschliche Genom aus Sicht der Bioinformatik Prof. Dr. Antje Krause FH Bingen a.krause@fh-bingen.de Kurzer Ausflug in die Genetik DNA (Desoxyribonukleinsäure)
Masterarbeit. Variantentolerantes Readmapping durch Locality Sensitive Hashing. Jens Quedenfeld November Gutachter: Sven Rahmann Dominik Köppl
 Masterarbeit Variantentolerantes Readmapping durch Locality Sensitive Hashing Jens Quedenfeld November 2015 Gutachter: Sven Rahmann Dominik Köppl Technische Universität Dortmund Fakultät für Informatik
Masterarbeit Variantentolerantes Readmapping durch Locality Sensitive Hashing Jens Quedenfeld November 2015 Gutachter: Sven Rahmann Dominik Köppl Technische Universität Dortmund Fakultät für Informatik
QTL-Mapping und Genomweite Assoziationsstudien
 QTL-Mapping und Genomweite Assoziationsstudien Birgit Gredler-Grandl Qualitas AG Birgit Gredler-Grandl Folien ZL I+II LFW C 27. Nov. 205 Prüfung 8.2.205 90 min, 09:5 0:45 Keine Hilfsmittel Nicht programmierbarer
QTL-Mapping und Genomweite Assoziationsstudien Birgit Gredler-Grandl Qualitas AG Birgit Gredler-Grandl Folien ZL I+II LFW C 27. Nov. 205 Prüfung 8.2.205 90 min, 09:5 0:45 Keine Hilfsmittel Nicht programmierbarer
Verbundvorhaben Fastwood
 Verbundvorhaben Fastwood Identifizierung kommerziell genutzter Pappelklone der Nutzen molekularer Marker für die Züchtung Hilke Schröder, Matthias Fladung (vti) Hintergrund Viele Arten der Gattung Populus
Verbundvorhaben Fastwood Identifizierung kommerziell genutzter Pappelklone der Nutzen molekularer Marker für die Züchtung Hilke Schröder, Matthias Fladung (vti) Hintergrund Viele Arten der Gattung Populus
Einführung Molekulare Bioinformatik
 Einführung Molekulare Bioinformatik Bernhard Haubold 22. Oktober 2013 Übersicht Was ist Bioinformatik? Kursstruktur Was ist Bioinformatik? Geschichtliche Entwicklung Information: Speicherung & Übertragung
Einführung Molekulare Bioinformatik Bernhard Haubold 22. Oktober 2013 Übersicht Was ist Bioinformatik? Kursstruktur Was ist Bioinformatik? Geschichtliche Entwicklung Information: Speicherung & Übertragung
Bioinformatik Für Biophysiker
 Bioinformatik Für Biophysiker Wintersemester 2006 / 2007 Ulf Leser Wissensmanagement in der Bioinformatik Wissensmanagement in der Bioinformatik Lehrstuhl seit 10/2002 Schwerpunkte Algorithmen der Bioinformatik
Bioinformatik Für Biophysiker Wintersemester 2006 / 2007 Ulf Leser Wissensmanagement in der Bioinformatik Wissensmanagement in der Bioinformatik Lehrstuhl seit 10/2002 Schwerpunkte Algorithmen der Bioinformatik
Grundideen der Gentechnik
 Grundideen der Gentechnik Die Gentechnik kombiniert Biotechnik und Züchtung. Wie in der Züchtung wird die Erbinformation eines Lebewesen verändert. Dabei nutzte man in den Anfängen der Gentechnik vor allem
Grundideen der Gentechnik Die Gentechnik kombiniert Biotechnik und Züchtung. Wie in der Züchtung wird die Erbinformation eines Lebewesen verändert. Dabei nutzte man in den Anfängen der Gentechnik vor allem
Schreibe ein Programm, das den AT Gehalt diese DNA Sequenz berechnet. Hinweis: A-Gehalt plus T-Gehalt bezogen auf die gesamte Sequenz.
 1 Einführung Keine Übungen 2 Python - Zeichenketten - "Strings" (1. Tag) 2.1 AT Gehalt berechnen Berechne aus der folgenden DNA Sequenz den AT-Gehalt. GAGATTTCTTTATTACAATCACTGTGTTTGTTAAAATACCTGCNTCACTTGGTTGTTCTTCAATAACACCAACTTA
1 Einführung Keine Übungen 2 Python - Zeichenketten - "Strings" (1. Tag) 2.1 AT Gehalt berechnen Berechne aus der folgenden DNA Sequenz den AT-Gehalt. GAGATTTCTTTATTACAATCACTGTGTTTGTTAAAATACCTGCNTCACTTGGTTGTTCTTCAATAACACCAACTTA
Zusammenfassung des 4. Abends
 Algorithmen in der Biologie Dr. Hans-Joachim Böckenhauer Dr. Dennis Komm Zusammenfassung des 4. Abends Zürich, 14. Mai 2014 1 DNA-Sequenzierung In diesem Abschnitt wollen wir einen kurzen Überblick geben
Algorithmen in der Biologie Dr. Hans-Joachim Böckenhauer Dr. Dennis Komm Zusammenfassung des 4. Abends Zürich, 14. Mai 2014 1 DNA-Sequenzierung In diesem Abschnitt wollen wir einen kurzen Überblick geben
Trio-Analyse (Exome-Seq)
 WS2017/2018 MSc Modul 7A Genomforschung und Sequenzanalyse - Einführung in Methoden der Bioinformatik- AG Hankeln Trio-Analyse (Exome-Seq) Mutationen mit Krankheitsrelevanz im Humangenom More than 3800
WS2017/2018 MSc Modul 7A Genomforschung und Sequenzanalyse - Einführung in Methoden der Bioinformatik- AG Hankeln Trio-Analyse (Exome-Seq) Mutationen mit Krankheitsrelevanz im Humangenom More than 3800
Übungsblatt Molekularbiologie und Genetik für Studierende der Bioinformatik II 1. Übung
 Übungsblatt Molekularbiologie und Genetik für Studierende der Bioinformatik II 1 Name des Studierenden: Datum: Einführung Übung Bitte bereiten Sie folgende Probleme vor der Übung am Mittwoch. Die Klausur
Übungsblatt Molekularbiologie und Genetik für Studierende der Bioinformatik II 1 Name des Studierenden: Datum: Einführung Übung Bitte bereiten Sie folgende Probleme vor der Übung am Mittwoch. Die Klausur
Hitze- und Trockentoleranz bei Gerste
 Projektverbund Strategien zur Anpassung von Kulturpflanzen an den Klimawandel Projektpräsentation Hitze- und Trockentoleranz bei Gerste Prof. Dr. Uwe Sonnewald Friedrich-Alexander-Universität Erlangen-Nürnberg
Projektverbund Strategien zur Anpassung von Kulturpflanzen an den Klimawandel Projektpräsentation Hitze- und Trockentoleranz bei Gerste Prof. Dr. Uwe Sonnewald Friedrich-Alexander-Universität Erlangen-Nürnberg
Wann sind Codes eindeutig entschlüsselbar?
 Wann sind Codes eindeutig entschlüsselbar? Definition Suffix Sei C ein Code. Ein Folge s {0, 1} heißt Suffix in C falls 1 c i, c j C : c i = c j s oder 2 c C und einen Suffix s in C: s = cs oder 3 c C
Wann sind Codes eindeutig entschlüsselbar? Definition Suffix Sei C ein Code. Ein Folge s {0, 1} heißt Suffix in C falls 1 c i, c j C : c i = c j s oder 2 c C und einen Suffix s in C: s = cs oder 3 c C
Humane Genotyp-Phänotyp-Datenbanken: Ein Statusbericht
 Workshop: Datenbank genomischer Varianten für die klinische Anwendung und die medizinische Forschung Essen 19. März 2014 Humane Genotyp-Phänotyp-Datenbanken: Ein Statusbericht Thomas Bettecken Max-Planck-Institut
Workshop: Datenbank genomischer Varianten für die klinische Anwendung und die medizinische Forschung Essen 19. März 2014 Humane Genotyp-Phänotyp-Datenbanken: Ein Statusbericht Thomas Bettecken Max-Planck-Institut
DATENSTRUKTUREN UND ALGORITHMEN
 DATENSTRUKTUREN UND ALGORITHMEN 2 Ist die Datenstruktur so wichtig??? Wahl der Datenstruktur wichtiger Schritt beim Entwurf und der Implementierung von Algorithmen Dünn besetzte Graphen und Matrizen bilden
DATENSTRUKTUREN UND ALGORITHMEN 2 Ist die Datenstruktur so wichtig??? Wahl der Datenstruktur wichtiger Schritt beim Entwurf und der Implementierung von Algorithmen Dünn besetzte Graphen und Matrizen bilden
Informatik II, SS 2018
 Informatik II - SS 2018 (Algorithmen & Datenstrukturen) Vorlesung 20 (9.7.2018) String Matching (Textsuche) Algorithmen und Komplexität Textsuche / String Matching Gegeben: Zwei Zeichenketten (Strings)
Informatik II - SS 2018 (Algorithmen & Datenstrukturen) Vorlesung 20 (9.7.2018) String Matching (Textsuche) Algorithmen und Komplexität Textsuche / String Matching Gegeben: Zwei Zeichenketten (Strings)
MODULE für den SCHULKOFFER GENTECHNIK
 MODULE für den SCHULKOFFER GENTECHNIK Modul 1 - DNA-Bastel-Set Zusammenbau eines Papiermodells in Form einer Doppelhelix sehr einfach, Unterstufe, ohne Koffer möglich Modul 2 - DNA-Isolierung aus Gemüse
MODULE für den SCHULKOFFER GENTECHNIK Modul 1 - DNA-Bastel-Set Zusammenbau eines Papiermodells in Form einer Doppelhelix sehr einfach, Unterstufe, ohne Koffer möglich Modul 2 - DNA-Isolierung aus Gemüse
Übung 2 Algorithmische Bioinformatik WS 15/16. Yvonne Mayer
 Übung 2 Algorithmische Bioinformatik WS 15/16 Yvonne Mayer Lösungen/ Wettbewerb Übung 1 Yvonne Mayer Übungen Algorithmische Bioinformatik WS 15/16 2 Lösungen Übung 1 vorstellen Fasta Sequenzen einlesen
Übung 2 Algorithmische Bioinformatik WS 15/16 Yvonne Mayer Lösungen/ Wettbewerb Übung 1 Yvonne Mayer Übungen Algorithmische Bioinformatik WS 15/16 2 Lösungen Übung 1 vorstellen Fasta Sequenzen einlesen
https://cuvillier.de/de/shop/publications/4021
 Jürgen Henrich (Autor) Erstellung segmentspezifischer molekularer Marker mittels Mikrodissektion und physikalische Kartierung der Resistenz gegen Schadinsekten (Diatraea spp.) bei tropischem Mais (Zea
Jürgen Henrich (Autor) Erstellung segmentspezifischer molekularer Marker mittels Mikrodissektion und physikalische Kartierung der Resistenz gegen Schadinsekten (Diatraea spp.) bei tropischem Mais (Zea
4.9.7 Konstruktion der Suffixbäume
 .9.7 Konstruktion der Suffixbäume Beipiel: xabxa (siehe Abbildung.27) Man beginnt mit der Konstruktion eines Suffixbaumes für gesamten String und schreibt eine 1 am Blatt, weil der Suffix xabxa an der
.9.7 Konstruktion der Suffixbäume Beipiel: xabxa (siehe Abbildung.27) Man beginnt mit der Konstruktion eines Suffixbaumes für gesamten String und schreibt eine 1 am Blatt, weil der Suffix xabxa an der
Vertiefendes Seminar zur Vorlesung Biochemie I
 Vertiefendes Seminar zur Vorlesung Biochemie I 30.01.2015 Klausurvorbereitung: Gerhild van Echten-Deckert Rekombinante DNA Fon. +49-228-732703 Homepage: http://www.limes.uni-bonn.de Klärung einiger Begriffe:
Vertiefendes Seminar zur Vorlesung Biochemie I 30.01.2015 Klausurvorbereitung: Gerhild van Echten-Deckert Rekombinante DNA Fon. +49-228-732703 Homepage: http://www.limes.uni-bonn.de Klärung einiger Begriffe:
Pharmazeutische Biologie WS2011/2012. Das neue Paradigma: Personalisierte Medizin
 2. Vorlesung Pharmazeutische Biologie WS2011/2012 Das neue Paradigma: Personalisierte Medizin Prof. Theo Dingermann Institut für Pharmazeutische Biologie Biozentrum Max-von Laue-Str. 9 60438 Frankfurt
2. Vorlesung Pharmazeutische Biologie WS2011/2012 Das neue Paradigma: Personalisierte Medizin Prof. Theo Dingermann Institut für Pharmazeutische Biologie Biozentrum Max-von Laue-Str. 9 60438 Frankfurt
Restriktion und Gentechnik
 Restriktion und Gentechnik Einteilung 1.) Restriktion - Restriktionsenzyme - Southern Blotting 2.)Gentechnik - sticky ends - blunt ends Restriktion Grundwerkzeuge der Gentechnik - Restriktionsenzymanalyse
Restriktion und Gentechnik Einteilung 1.) Restriktion - Restriktionsenzyme - Southern Blotting 2.)Gentechnik - sticky ends - blunt ends Restriktion Grundwerkzeuge der Gentechnik - Restriktionsenzymanalyse
Python im Bioinformatiker-Alltag
 Python im Bioinformatiker-Alltag Marcel Martin Bioinformatik für Hochdurchsatztechnologien, TU Dortmund 6. Oktober 2011 1 von 27 Worum gehts? Bioinformatik Löst Probleme in Biologie oder Medizin Teilbereich
Python im Bioinformatiker-Alltag Marcel Martin Bioinformatik für Hochdurchsatztechnologien, TU Dortmund 6. Oktober 2011 1 von 27 Worum gehts? Bioinformatik Löst Probleme in Biologie oder Medizin Teilbereich
Pharmazeutische Biologie WS2011/2012. Das neue Paradigma: Personalisierte Medizin
 3. Vorlesung Pharmazeutische Biologie WS2011/2012 Das neue Paradigma: Personalisierte Medizin Prof. Theo Dingermann Institut für Pharmazeutische Biologie Biozentrum Max-von Laue-Str. 9 60438 Frankfurt
3. Vorlesung Pharmazeutische Biologie WS2011/2012 Das neue Paradigma: Personalisierte Medizin Prof. Theo Dingermann Institut für Pharmazeutische Biologie Biozentrum Max-von Laue-Str. 9 60438 Frankfurt
C SB. Genomics Herausforderungen und Chancen. Genomics. Genomic data. Prinzipien dominieren über Detail-Fluten. in 10 Minuten!
 Genomics Herausforderungen und Chancen Prinzipien dominieren über Detail-Fluten Genomics in 10 Minuten! biol. Prin cip les Genomic data Dr.Thomas WERNER Scientific & Business Consulting +49 89 81889252
Genomics Herausforderungen und Chancen Prinzipien dominieren über Detail-Fluten Genomics in 10 Minuten! biol. Prin cip les Genomic data Dr.Thomas WERNER Scientific & Business Consulting +49 89 81889252
Quelle Gen: GK-120F
 1 Einführung Keine Übungen 2 Python - Zeichenketten - "Strings" (1. Tag) 2.1 AT Gehalt berechnen Berechne aus der folgenden DNA Sequenz den AT-Gehalt. GAGATTTCTTTATTACAATCACTGTGTTTGTTAAAATACCTGCNTCACTTGGTTGTTCTTCAATAACACCAACTTA
1 Einführung Keine Übungen 2 Python - Zeichenketten - "Strings" (1. Tag) 2.1 AT Gehalt berechnen Berechne aus der folgenden DNA Sequenz den AT-Gehalt. GAGATTTCTTTATTACAATCACTGTGTTTGTTAAAATACCTGCNTCACTTGGTTGTTCTTCAATAACACCAACTTA
Übung 1 Algorithmische Bioinformatik WS 15/16. Yvonne Mayer
 Übung 1 Algorithmische Bioinformatik WS 15/16 Yvonne Mayer Allgemeines Yvonne Mayer Übungen Algorithmische Bioinformatik WS 15/16 2 Ablauf der Übung Insgesamt 7 Übungszettel Abgabe in Gruppen von 2 Personen
Übung 1 Algorithmische Bioinformatik WS 15/16 Yvonne Mayer Allgemeines Yvonne Mayer Übungen Algorithmische Bioinformatik WS 15/16 2 Ablauf der Übung Insgesamt 7 Übungszettel Abgabe in Gruppen von 2 Personen
Das internationale Human-Genom Projekt. Stand Ergebnisse Perspektiven
 Das internationale Human-Genom Projekt Stand Ergebnisse Perspektiven 2003 1953 April, 25 th, 1953 Watson, J.D., and F.H.C.Crick. 1953. Molecular Structure of Nucleic Acids: A Structure for Deoxynucleic
Das internationale Human-Genom Projekt Stand Ergebnisse Perspektiven 2003 1953 April, 25 th, 1953 Watson, J.D., and F.H.C.Crick. 1953. Molecular Structure of Nucleic Acids: A Structure for Deoxynucleic
Algorithmus Sortieren von Zahlen (aufsteigend)
 Hausaufgabe https://de.wikipedia.org/wiki/dualsystem http://de.wikipedia.org/ieee_754 (Darstellung von Gleitkommazahlen) http://de.wikipedia.org/wiki/wurzel_(mat hematik)#berechnung - lesen, verstehen
Hausaufgabe https://de.wikipedia.org/wiki/dualsystem http://de.wikipedia.org/ieee_754 (Darstellung von Gleitkommazahlen) http://de.wikipedia.org/wiki/wurzel_(mat hematik)#berechnung - lesen, verstehen
Aufgabe 7: Distanzbasierte Phylogenie: Neighbor Joining. Stefan Kröger, Philippe Thomas Wissensmanagement in der Bioinformatik
 Aufgabe 7: Distanzbasierte Phylogenie: Neighbor Joining Stefan Kröger, Philippe Thomas Wissensmanagement in der Bioinformatik Daten Wir verwenden neue Daten Die müssen sie ausnahmsweise selber suchen DNA-Sequenzen
Aufgabe 7: Distanzbasierte Phylogenie: Neighbor Joining Stefan Kröger, Philippe Thomas Wissensmanagement in der Bioinformatik Daten Wir verwenden neue Daten Die müssen sie ausnahmsweise selber suchen DNA-Sequenzen
Einführung Molekulare Bioinformatik
 Einführung Molekulare Bioinformatik Bernhard Haubold 21. Oktober 2014 Übersicht Was ist Bioinformatik? Kursstruktur Was ist Bioinformatik? Geschichtliche Entwicklung Information: Speicherung & Übertragung
Einführung Molekulare Bioinformatik Bernhard Haubold 21. Oktober 2014 Übersicht Was ist Bioinformatik? Kursstruktur Was ist Bioinformatik? Geschichtliche Entwicklung Information: Speicherung & Übertragung
Algorithmen und Datenstrukturen SS Übungsblatt 9: Suchen
 Ludwig-Maximilians-Universität München München, 05.06.2018 Institut für Informatik Prof. Dr. Thomas Seidl Anna Beer, Florian Richter Algorithmen und Datenstrukturen SS 2018 Übungsblatt 9: Suchen Tutorien:
Ludwig-Maximilians-Universität München München, 05.06.2018 Institut für Informatik Prof. Dr. Thomas Seidl Anna Beer, Florian Richter Algorithmen und Datenstrukturen SS 2018 Übungsblatt 9: Suchen Tutorien:
Informatik II, SS 2018
 Informatik II - SS 2018 (Algorithmen & Datenstrukturen) Vorlesung 21 (11.7.2018) String Matching (Textsuche) II Greedy Algorithmen I Algorithmen und Komplexität Textsuche / String Matching Gegeben: Zwei
Informatik II - SS 2018 (Algorithmen & Datenstrukturen) Vorlesung 21 (11.7.2018) String Matching (Textsuche) II Greedy Algorithmen I Algorithmen und Komplexität Textsuche / String Matching Gegeben: Zwei
Sequenziertechnologien
 Sequenziertechnologien Folien teilweise von G. Thallinger übernommen 11 Entwicklung der Sequenziertechnologie First Generation 1977 Sanger Sequenzierung (GOLD Standard) Second Generation 2005 454 Sequencing
Sequenziertechnologien Folien teilweise von G. Thallinger übernommen 11 Entwicklung der Sequenziertechnologie First Generation 1977 Sanger Sequenzierung (GOLD Standard) Second Generation 2005 454 Sequencing
Übung 9. a) In welchem Teil eines Operons führen Mutationen zur Veränderungen der produzierten Menge eines Enzyms?
 Bitte schreiben Sie Ihre Antworten direkt auf das Übungsblatt. Falls Sie mehr Platz brauchen verweisen Sie auf Zusatzblätter. Vergessen Sie Ihren Namen nicht! Abgabe der Übung bis spätestens 19. 05. 08-16:30
Bitte schreiben Sie Ihre Antworten direkt auf das Übungsblatt. Falls Sie mehr Platz brauchen verweisen Sie auf Zusatzblätter. Vergessen Sie Ihren Namen nicht! Abgabe der Übung bis spätestens 19. 05. 08-16:30
Genkartierung durch Rekombination in Drosophila. Chapter 4 Opener
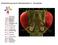 Genkartierung durch Rekombination in Drosophila Chapter 4 Opener Gekoppelte Allele werden zusammen vererbt n Figure 4-2 Crossing-Over erzeugt neue Allel-Kombinationen Figure 4-3 Crossover zwischen Chromatiden
Genkartierung durch Rekombination in Drosophila Chapter 4 Opener Gekoppelte Allele werden zusammen vererbt n Figure 4-2 Crossing-Over erzeugt neue Allel-Kombinationen Figure 4-3 Crossover zwischen Chromatiden
Bioinformatik I: Grundlagen der Gentechnik
 Bioinformatik I: Grundlagen der Gentechnik Dr. Maik Böhmer Institut für Biologie und Biotechnologie der Pflanzen Schlossplatz 7 Schwerpunkte: Vorlesung 1: Einführung & Enzyme der Gentechnik Vorlesung 2:
Bioinformatik I: Grundlagen der Gentechnik Dr. Maik Böhmer Institut für Biologie und Biotechnologie der Pflanzen Schlossplatz 7 Schwerpunkte: Vorlesung 1: Einführung & Enzyme der Gentechnik Vorlesung 2:
Wie halten neue Technologien Einzug in unser Leben und welche Auswirkungen kann dies haben?
 Wie halten neue Technologien Einzug in unser Leben und welche Auswirkungen kann dies haben? Prof. Dr. (TU NN) Norbert Pohlmann Institut für Internet-Sicherheit if(is) Westfälische Hochschule, Gelsenkirchen
Wie halten neue Technologien Einzug in unser Leben und welche Auswirkungen kann dies haben? Prof. Dr. (TU NN) Norbert Pohlmann Institut für Internet-Sicherheit if(is) Westfälische Hochschule, Gelsenkirchen
Genomprojekte und die Kartierung des menschlichen Genoms
 Genomprojekte und die Kartierung des menschlichen Genoms Peter N. Robinson Institut für medizinische Genetik Charité Universitätsmedizin Berlin 12. November 2014 Peter N. Robinson (Charité) Kartierung
Genomprojekte und die Kartierung des menschlichen Genoms Peter N. Robinson Institut für medizinische Genetik Charité Universitätsmedizin Berlin 12. November 2014 Peter N. Robinson (Charité) Kartierung
Aufgabe 6: Distanzbasierte Phylogenie: Hierarchisches Clustering. Ulf Leser Wissensmanagement in der Bioinformatik
 Aufgabe 6: Distanzbasierte Phylogenie: Hierarchisches Clustering Ulf Leser Wissensmanagement in der Bioinformatik Daten Wir verwenden neue Daten Die müssen sie ausnahmsweise selber suchen DNA-Sequenzen
Aufgabe 6: Distanzbasierte Phylogenie: Hierarchisches Clustering Ulf Leser Wissensmanagement in der Bioinformatik Daten Wir verwenden neue Daten Die müssen sie ausnahmsweise selber suchen DNA-Sequenzen
Informatik II, SS 2016
 Informatik II - SS 2016 (Algorithmen & Datenstrukturen) Vorlesung 20 (13.7.2016) String Matching (Textsuche) Algorithmen und Komplexität Textsuche / String Matching Gegeben: Zwei Zeichenketten (Strings)
Informatik II - SS 2016 (Algorithmen & Datenstrukturen) Vorlesung 20 (13.7.2016) String Matching (Textsuche) Algorithmen und Komplexität Textsuche / String Matching Gegeben: Zwei Zeichenketten (Strings)
Informatik II, SS 2014
 Informatik II SS 2014 (Algorithmen & Datenstrukturen) Vorlesung 20 (23.7.2014) All Pairs Shortest Paths, String Matching (Textsuche) Algorithmen und Komplexität Vorlesungsevaluation Sie sollten alle eine
Informatik II SS 2014 (Algorithmen & Datenstrukturen) Vorlesung 20 (23.7.2014) All Pairs Shortest Paths, String Matching (Textsuche) Algorithmen und Komplexität Vorlesungsevaluation Sie sollten alle eine
Molekularbiologische Datenbanken
 Molekularbiologische Datenbanken Kartierung von Chromsomen I Biotechnische Grundlagen Ulf Leser Wissensmanagement in der Bioinformatik Ankündigung Am 2.6.2004 (nächste Woche) beginnt die Vorlesung um 9.00
Molekularbiologische Datenbanken Kartierung von Chromsomen I Biotechnische Grundlagen Ulf Leser Wissensmanagement in der Bioinformatik Ankündigung Am 2.6.2004 (nächste Woche) beginnt die Vorlesung um 9.00
Algorithmische Bioinformatik I (IN5000)
 Algorithmische Bioinformatik I (IN5000) Title Algorithmic Bioinformatics I Typ Vorlesung mit Übungen Credits 9 Lehrform/SWS 4V + 2Ü Sprache Deutsch oder Englisch (wird vom Dozenten zum Vorlesungsbeginn
Algorithmische Bioinformatik I (IN5000) Title Algorithmic Bioinformatics I Typ Vorlesung mit Übungen Credits 9 Lehrform/SWS 4V + 2Ü Sprache Deutsch oder Englisch (wird vom Dozenten zum Vorlesungsbeginn
Thema Gentechnologie. Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #
 Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #2 06. 05. 2014 Restriktionsenzyme (http://rebase.neb.com) Statistik:Enzymes: Total: 15093 Restriction Enzymes 3945 Type I
Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #2 06. 05. 2014 Restriktionsenzyme (http://rebase.neb.com) Statistik:Enzymes: Total: 15093 Restriction Enzymes 3945 Type I
Effizienter Planaritätstest Vorlesung am
 Effizienter Planaritätstest Vorlesung am 23.04.2014 INSTITUT FÜR THEORETISCHE INFORMATIK PROF. DR. DOROTHEA WAGNER Satz Gegebenen einen Graphen G = (V, E) mit n Kanten und m Knoten, kann in O(n + m) Zeit
Effizienter Planaritätstest Vorlesung am 23.04.2014 INSTITUT FÜR THEORETISCHE INFORMATIK PROF. DR. DOROTHEA WAGNER Satz Gegebenen einen Graphen G = (V, E) mit n Kanten und m Knoten, kann in O(n + m) Zeit
Algorithmische Geometrie: Einstimmung
 Algorithmische Geometrie: Einstimmung Nico Düvelmeyer WS 2009/2010, 20.10.2009 Überblick 1 Organisatorisches 2 Fachgebiet Typische Untersuchungsgegenstände Typische Anwendungsgebiete 3 Inhalte der Vorlesung
Algorithmische Geometrie: Einstimmung Nico Düvelmeyer WS 2009/2010, 20.10.2009 Überblick 1 Organisatorisches 2 Fachgebiet Typische Untersuchungsgegenstände Typische Anwendungsgebiete 3 Inhalte der Vorlesung
Algorithmen auf Sequenzen
 Algorithmen auf Sequenzen Fehlertolerante Mustersuche: Distanz- und Ähnlichkeitsmaße Sven Rahmann Genominformatik Universitätsklinikum Essen Universität Duisburg-Essen Universitätsallianz Ruhr Einführung
Algorithmen auf Sequenzen Fehlertolerante Mustersuche: Distanz- und Ähnlichkeitsmaße Sven Rahmann Genominformatik Universitätsklinikum Essen Universität Duisburg-Essen Universitätsallianz Ruhr Einführung
Informatik II, SS 2014
 Informatik II SS 2014 (Algorithmen & Datenstrukturen) Vorlesung 11 (4.6.2014) Binäre Suchbäume II Algorithmen und Komplexität Binäre Suchbäume Binäre Suchbäume müssen nicht immer so schön symmetrisch sein
Informatik II SS 2014 (Algorithmen & Datenstrukturen) Vorlesung 11 (4.6.2014) Binäre Suchbäume II Algorithmen und Komplexität Binäre Suchbäume Binäre Suchbäume müssen nicht immer so schön symmetrisch sein
Beispiel Gröbnerbasen-Berechnung
 Beispiel Gröbnerbasen-Berechnung Bsp: Seien f 1 = x 2 y + xy, f 2 = xy 2 + 1 R[x, y] in grlex-ordnung. S(f 1, f 2 ) = yf 1 xf 2 = xy 2 x. Division liefert S(f 1, f 2 ) = 1 f 2 x 1. Wir fügen f 3 = x 1
Beispiel Gröbnerbasen-Berechnung Bsp: Seien f 1 = x 2 y + xy, f 2 = xy 2 + 1 R[x, y] in grlex-ordnung. S(f 1, f 2 ) = yf 1 xf 2 = xy 2 x. Division liefert S(f 1, f 2 ) = 1 f 2 x 1. Wir fügen f 3 = x 1
Alignment-Verfahren zum Vergleich biologischer Sequenzen
 zum Vergleich biologischer Sequenzen Hans-Joachim Böckenhauer Dennis Komm Volkshochschule Zürich. April Ein biologisches Problem Fragestellung Finde eine Methode zum Vergleich von DNA-Molekülen oder Proteinen
zum Vergleich biologischer Sequenzen Hans-Joachim Böckenhauer Dennis Komm Volkshochschule Zürich. April Ein biologisches Problem Fragestellung Finde eine Methode zum Vergleich von DNA-Molekülen oder Proteinen
Informatik II, SS 2018
 Informatik II - SS 2018 (Algorithmen & Datenstrukturen) Vorlesung 19 (27.6.2018) Dynamische Programmierung III Algorithmen und Komplexität Dynamische Programmierung DP Rekursion + Memoization Memoize:
Informatik II - SS 2018 (Algorithmen & Datenstrukturen) Vorlesung 19 (27.6.2018) Dynamische Programmierung III Algorithmen und Komplexität Dynamische Programmierung DP Rekursion + Memoization Memoize:
Kapitel 3: Untere Schranken für algorithmische Probleme Gliederung
 Gliederung 1. Grundlagen 2. Analyse der Laufzeit von Algorithmen 3. Untere Schranken für algorithmische Probleme 4. Sortier- und Selektionsverfahren 5. Paradigmen des Algorithmenentwurfs 6. Ausgewählte
Gliederung 1. Grundlagen 2. Analyse der Laufzeit von Algorithmen 3. Untere Schranken für algorithmische Probleme 4. Sortier- und Selektionsverfahren 5. Paradigmen des Algorithmenentwurfs 6. Ausgewählte
Quiz zum Praktikum Tierartendifferenzierung
 Quiz zum Praktikum Tierartendifferenzierung Frage 1: Aus welcher DNA wurden am Praktikumstag die Abschnitte für die Tierartenbestimmung untersucht? A. DNA aus dem Zellkern B. Mitochondriale DNA C. Plasmid-DNA
Quiz zum Praktikum Tierartendifferenzierung Frage 1: Aus welcher DNA wurden am Praktikumstag die Abschnitte für die Tierartenbestimmung untersucht? A. DNA aus dem Zellkern B. Mitochondriale DNA C. Plasmid-DNA
Algorithms for analyzing signals in DNA Applications to transcription and translation
 Research Collection Doctoral Thesis Algorithms for analyzing signals in DNA Applications to transcription and translation Author(s): Friberg, Markus Publication Date: 2007 Permanent Link: https://doi.org/10.3929/ethz-a-005378601
Research Collection Doctoral Thesis Algorithms for analyzing signals in DNA Applications to transcription and translation Author(s): Friberg, Markus Publication Date: 2007 Permanent Link: https://doi.org/10.3929/ethz-a-005378601
Liste MI / Liste I Programmieren in C++
 Liste MI / Liste I Programmieren in C++ Fachhochschule Wiesbaden, FB Design Informatik Medien Studiengang Medieninformatik WS 2007/2008 Kapitel 1-4 1 Ziele Kennenlernen einer weiteren objektorientierten
Liste MI / Liste I Programmieren in C++ Fachhochschule Wiesbaden, FB Design Informatik Medien Studiengang Medieninformatik WS 2007/2008 Kapitel 1-4 1 Ziele Kennenlernen einer weiteren objektorientierten
Thema Gentechnologie. Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #
 Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #1 21. 04. 2015 Amazon-Preis: EUR 36,95 Kostenlose Lieferung. letzte Auflage 2011. 5. September 2011 ISBN-10: 3827428688 ISBN-13:
Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #1 21. 04. 2015 Amazon-Preis: EUR 36,95 Kostenlose Lieferung. letzte Auflage 2011. 5. September 2011 ISBN-10: 3827428688 ISBN-13:
Algorithmen und Datenstrukturen
 Algorithmen und Datenstrukturen A3. Sortieren: Selection- und Insertionsort Marcel Lüthi and Gabriele Röger Universität Basel 1. März 2018 Sortieralgorithmen Inhalt dieser Veranstaltung A&D Sortieren Komplexitätsanalyse
Algorithmen und Datenstrukturen A3. Sortieren: Selection- und Insertionsort Marcel Lüthi and Gabriele Röger Universität Basel 1. März 2018 Sortieralgorithmen Inhalt dieser Veranstaltung A&D Sortieren Komplexitätsanalyse
Von der DNA zur Datenbank: Sequenzierung & Assemblierung
 Vorlesung Einführung in die Bioinforma4k SoSe 2012 Von der DN zur Datenbank: Sequenzierung & ssemblierung Prof. Daniel Huson ZBI enter for Bioinformatics Entdeckung der DN Friedrich Miescher (1844-1895)
Vorlesung Einführung in die Bioinforma4k SoSe 2012 Von der DN zur Datenbank: Sequenzierung & ssemblierung Prof. Daniel Huson ZBI enter for Bioinformatics Entdeckung der DN Friedrich Miescher (1844-1895)
Erster Baum genetisch sequenziert Genetische Veränderung geplant - Ökologen warnen vor Gentech- Pflanzen
 Erster Baum genetisch sequenziert Genetische Veränderung geplant - Ökologen warnen vor Gentech- Pflanzen Das erste Genom eines Baumes wurde nach Angaben des Wissenschaftsmagazins Science nun fertig entschlüsselt.
Erster Baum genetisch sequenziert Genetische Veränderung geplant - Ökologen warnen vor Gentech- Pflanzen Das erste Genom eines Baumes wurde nach Angaben des Wissenschaftsmagazins Science nun fertig entschlüsselt.
Polygone - Bausteine der Computergrafik
 Polygone - Bausteine der Computergrafik Schülerseminar Florian Buchegger Johannes Kepler Universität Linz Dez 12, 2014 Wo werden Polygone verwendet? Welche wichtige Algorithmen gibt es? Outline Wo werden
Polygone - Bausteine der Computergrafik Schülerseminar Florian Buchegger Johannes Kepler Universität Linz Dez 12, 2014 Wo werden Polygone verwendet? Welche wichtige Algorithmen gibt es? Outline Wo werden
A T C G G C T A A T A T
 Vorlesung*Einführung*in*die*Bioinforma4k*SoSe*2013* * Von*der*DNA*zur*Datenbank:* Sequenzierung*&*Assemblierung* * Prof.&Daniel&Huson& ZBIT Center for Bioinformatics Singapore Center on Environmental Life
Vorlesung*Einführung*in*die*Bioinforma4k*SoSe*2013* * Von*der*DNA*zur*Datenbank:* Sequenzierung*&*Assemblierung* * Prof.&Daniel&Huson& ZBIT Center for Bioinformatics Singapore Center on Environmental Life
molekularen Rinderzucht
 Möglichkeiten der molekularen Rinderzucht Johann Sölkner Gliederung Einleitung Molekulare Marker Suche nach wichtigen Genen Molekulare Zuchtwertschätzung Auswirkung auf Zuchtprogramme Versprechen der Molekulargenetiker
Möglichkeiten der molekularen Rinderzucht Johann Sölkner Gliederung Einleitung Molekulare Marker Suche nach wichtigen Genen Molekulare Zuchtwertschätzung Auswirkung auf Zuchtprogramme Versprechen der Molekulargenetiker
Inhaltsübersicht. Vorwort 15. Vorwort zur deutschen Ausgabe 22. Kapitel 1 Elemente der Programmierung 25. Kapitel 2 Funktionen und Module 203
 Inhaltsübersicht Vorwort 15 Vorwort zur deutschen Ausgabe 22 Kapitel 1 Elemente der Programmierung 25 Kapitel 2 Funktionen und Module 203 Kapitel 3 Objektorientierte Programmierung 335 Kapitel 4 Algorithmen
Inhaltsübersicht Vorwort 15 Vorwort zur deutschen Ausgabe 22 Kapitel 1 Elemente der Programmierung 25 Kapitel 2 Funktionen und Module 203 Kapitel 3 Objektorientierte Programmierung 335 Kapitel 4 Algorithmen
Genomanalyse Vorlesung Masterstudiengang 2011 Jena FLI. Klaus Huse Leibniz-Institut für Altersforschung Fritz-Lipmann-Institut Jena
 Vorlesung Masterstudiengang 2011 Jena 9.11.2011 FLI Klaus Huse Leibniz-Institut für Altersforschung Fritz-Lipmann-Institut Jena Genom Begriffsbestimmung Gen (Johannsen, 1909) - Erbfaktor, der eine einzelne
Vorlesung Masterstudiengang 2011 Jena 9.11.2011 FLI Klaus Huse Leibniz-Institut für Altersforschung Fritz-Lipmann-Institut Jena Genom Begriffsbestimmung Gen (Johannsen, 1909) - Erbfaktor, der eine einzelne
Vorbesprechung Seminar Biomedical Informatics
 Vorbesprechung Martin Dugas und Xiaoyi Jiang Institut für Informatik Sommersemester 2016 Organisation Vorlage: Englischsprachige Publikation Vortrag: ca. 30min + 15min Diskussion, Blockseminar Anfang/Mitte
Vorbesprechung Martin Dugas und Xiaoyi Jiang Institut für Informatik Sommersemester 2016 Organisation Vorlage: Englischsprachige Publikation Vortrag: ca. 30min + 15min Diskussion, Blockseminar Anfang/Mitte
2. Woche Eindeutige Entschlüsselbarleit, Sätze von Kraft und McMillan, Huffmancodierung
 2 Woche Eindeutige Entschlüsselbarleit, Sätze von Kraft und McMillan, Huffmancodierung 2 Woche: Eindeutige Entschlüsselbarleit, Sätze von Kraft und McMillan, Huffmancodierung 24/ 44 Zwei Beispiele a 0
2 Woche Eindeutige Entschlüsselbarleit, Sätze von Kraft und McMillan, Huffmancodierung 2 Woche: Eindeutige Entschlüsselbarleit, Sätze von Kraft und McMillan, Huffmancodierung 24/ 44 Zwei Beispiele a 0
B I O T E C H N O L O G I E. Molekulare Biotechnologie Engineering von Biosystemen. Bioprozesstechnik Engineering von Produktionsverfahren
 B I O T E C H N O L O G I E Molekulare Biotechnologie Engineering von Biosystemen Zell-Engineering Stoffwechsel-Engineering Protein-Engineering Integrierte Vernetzung Bioprozesstechnik Engineering von
B I O T E C H N O L O G I E Molekulare Biotechnologie Engineering von Biosystemen Zell-Engineering Stoffwechsel-Engineering Protein-Engineering Integrierte Vernetzung Bioprozesstechnik Engineering von
ATTGACTTTGGACTAGAATCGATAAAATCCGCATCATCATACCCATTGGCCGGGTAACCCTG TCATGTCATTTAGGGATTTTTATTTTTAAAACGTATTATGGACCACAGGATCATGATCATGAC
 ATTGACTTTGGACTAGAATCGATAAAATCCGCATCATCATACCCATTGGCCGGGTAACCCTG ACGATTAGTCATCATGAGGGACTGGTTTAGGTTTCCACATGACGTATGCATTAAACCCTTTAG TGGAGGGTTTGGGGCCCATTCATGATCTCTCTCAAGGAGATACGATCATGTCCCCCCTTTTGG ACGTATGACTAAGGCCTACCATGGGACTGGTCAGTCATGCATGACATAGACTGGTACCATTT
ATTGACTTTGGACTAGAATCGATAAAATCCGCATCATCATACCCATTGGCCGGGTAACCCTG ACGATTAGTCATCATGAGGGACTGGTTTAGGTTTCCACATGACGTATGCATTAAACCCTTTAG TGGAGGGTTTGGGGCCCATTCATGATCTCTCTCAAGGAGATACGATCATGTCCCCCCTTTTGG ACGTATGACTAAGGCCTACCATGGGACTGGTCAGTCATGCATGACATAGACTGGTACCATTT
Themenübersicht Verwendung im Studium Voraussetzungen Ziele Website zum Buch Danksagungen... 21
 Vorwort 15 Themenübersicht... 15 Verwendung im Studium... 17 Voraussetzungen... 18 Ziele.... 19 Website zum Buch... 20 Danksagungen... 21 Vorwort zur deutschen Ausgabe 22 Übersetzung... 22 Verwendung in
Vorwort 15 Themenübersicht... 15 Verwendung im Studium... 17 Voraussetzungen... 18 Ziele.... 19 Website zum Buch... 20 Danksagungen... 21 Vorwort zur deutschen Ausgabe 22 Übersetzung... 22 Verwendung in
Gentechnische Methoden
 Desmond S. T. Nicholl Gentechnische Methoden 2. Auflage Aus dem Englischen übersetzt von Renate FitzRoy und Kurt Beginnen Spektrum Akademischer Verlag Heidelberg Berlin Inhalt Vorwort XI 1. 1.1 1.2 1.3
Desmond S. T. Nicholl Gentechnische Methoden 2. Auflage Aus dem Englischen übersetzt von Renate FitzRoy und Kurt Beginnen Spektrum Akademischer Verlag Heidelberg Berlin Inhalt Vorwort XI 1. 1.1 1.2 1.3
Aufgaben zur Klausurvorbereitung
 Vorlesung Graphen und Optimierung Sommersemester 2013/14 Prof. S. Lange Aufgaben zur Klausurvorbereitung Hier finden Sie eine Reihe von Übungsaufgaben, die wir an den beiden Vorlesungsterminen am 29.01.2014
Vorlesung Graphen und Optimierung Sommersemester 2013/14 Prof. S. Lange Aufgaben zur Klausurvorbereitung Hier finden Sie eine Reihe von Übungsaufgaben, die wir an den beiden Vorlesungsterminen am 29.01.2014
3.5 Moderne Genetik - Vorgänge
 3.5 Moderne Genetik - Vorgänge Der genetische Code Jedes Gen besteht aus sogenannten Basentriplets. Das ist eine Sequenz von drei aufeinanderfolgenden Nukleinbasen, die für eine bestimmte Aminosäure stehen.
3.5 Moderne Genetik - Vorgänge Der genetische Code Jedes Gen besteht aus sogenannten Basentriplets. Das ist eine Sequenz von drei aufeinanderfolgenden Nukleinbasen, die für eine bestimmte Aminosäure stehen.
Qualitatives räumliches Schließen zur Objektverfolgung in Bildfolgen
 - Diplomarbeit - Qualitatives räumliches Schließen zur Objektverfolgung in Bildfolgen Enrico Ehrich Fachhochschule Brandenburg 2003 Aufgabe Konzeption eines Systems zur Verfolgung von Objekten in Bildfolgen
- Diplomarbeit - Qualitatives räumliches Schließen zur Objektverfolgung in Bildfolgen Enrico Ehrich Fachhochschule Brandenburg 2003 Aufgabe Konzeption eines Systems zur Verfolgung von Objekten in Bildfolgen
Molekulare Klonierung Praktikum
 Molekulare Klonierung Praktikum 2013 Praktikumsaufgabe Ligation 1. Zusammensetzung des Ligationsreaktions-ansatzes : 1 l Vektor DNA 1 l Insert DNA 2 l 10X Ligase Puffer 15 l destillertes Wasser 1 l Ligase
Molekulare Klonierung Praktikum 2013 Praktikumsaufgabe Ligation 1. Zusammensetzung des Ligationsreaktions-ansatzes : 1 l Vektor DNA 1 l Insert DNA 2 l 10X Ligase Puffer 15 l destillertes Wasser 1 l Ligase
KEINE ANGST VOR OPEN ACCESS
 KEINE ANGST VOR OPEN ACCESS Workshop Möglichkeiten der Sichtbarkeitssteigerung in den Geistes-, Sozial- und Kulturwissenschaften, Uni Wien, 7.5.2015 Guido Blechl, Open Access Office der UB-Wien Diese Präsentation
KEINE ANGST VOR OPEN ACCESS Workshop Möglichkeiten der Sichtbarkeitssteigerung in den Geistes-, Sozial- und Kulturwissenschaften, Uni Wien, 7.5.2015 Guido Blechl, Open Access Office der UB-Wien Diese Präsentation
Informatik II, SS 2014
 Informatik II SS 2014 (Algorithmen & Datenstrukturen) Vorlesung 21 (29.7.2014) String Matching (Textsuche) II Algorithmen und Komplexität Textsuche / String Matching Gegeben: Zwei Zeichenketten (Strings)
Informatik II SS 2014 (Algorithmen & Datenstrukturen) Vorlesung 21 (29.7.2014) String Matching (Textsuche) II Algorithmen und Komplexität Textsuche / String Matching Gegeben: Zwei Zeichenketten (Strings)
Informatik II, SS 2016
 Informatik II - SS 2016 (Algorithmen & Datenstrukturen) Vorlesung 21 (15.7.2016) String Matching (Textsuche) Approximate String Matching Algorithmen und Komplexität Textsuche / String Matching Gegeben:
Informatik II - SS 2016 (Algorithmen & Datenstrukturen) Vorlesung 21 (15.7.2016) String Matching (Textsuche) Approximate String Matching Algorithmen und Komplexität Textsuche / String Matching Gegeben:
GroupSeq++/GWAS. Ein R-Programmpaket zur Optimierung und flexiblen Anpassung von Mehrstufen-Designs für genomweite Assoziationsstudien
 GroupSeq++/GWAS Ein R-Programmpaket zur Optimierung und flexiblen Anpassung von Mehrstufen-Designs für genomweite Assoziationsstudien Impressum TMF Technologie- und Methodenplattform für die vernetzte
GroupSeq++/GWAS Ein R-Programmpaket zur Optimierung und flexiblen Anpassung von Mehrstufen-Designs für genomweite Assoziationsstudien Impressum TMF Technologie- und Methodenplattform für die vernetzte
Praktische Informatik I
 Praktische Informatik I WS 2005/2005 Prof. Dr. Wolfgang Effelsberg Lehrstuhl für Praktische Informatik IV Universität Mannheim 1. Einführung 1-1 Inhaltsverzeichnis (1) 1. Einführung 1.1 Was ist Informatik?
Praktische Informatik I WS 2005/2005 Prof. Dr. Wolfgang Effelsberg Lehrstuhl für Praktische Informatik IV Universität Mannheim 1. Einführung 1-1 Inhaltsverzeichnis (1) 1. Einführung 1.1 Was ist Informatik?
AlgoBio WS 16/17 Protein-DNA Interaktionen ChiP-Seq Datenanalyse. Annalisa Marsico
 AlgoBio WS 16/17 Protein-DNA Interaktionen ChiP-Seq Datenanalyse Annalisa Marsico 6.02.2017 Protein-DNA Interaktionen Häufig binden sich Proteine an DNA, um ihre biologische Funktion zu regulieren. Transkriptionsfaktoren
AlgoBio WS 16/17 Protein-DNA Interaktionen ChiP-Seq Datenanalyse Annalisa Marsico 6.02.2017 Protein-DNA Interaktionen Häufig binden sich Proteine an DNA, um ihre biologische Funktion zu regulieren. Transkriptionsfaktoren
Grundlagen der Programmierung (Vorlesung 24)
 Grundlagen der Programmierung (Vorlesung 24) Ralf Möller, FH-Wedel Vorige Vorlesung Anwendung im Bereich Compilerbau Inhalt dieser Vorlesung Turing-Maschinen Berechenbarkeitstheorie, Halteproblem Lernziele
Grundlagen der Programmierung (Vorlesung 24) Ralf Möller, FH-Wedel Vorige Vorlesung Anwendung im Bereich Compilerbau Inhalt dieser Vorlesung Turing-Maschinen Berechenbarkeitstheorie, Halteproblem Lernziele
Algorithmen und Datenstrukturen (ESE) Entwurf, Analyse und Umsetzung von Algorithmen (IEMS) WS 2014 / 2015 Vorlesung 14, Donnerstag, 5.
 Algorithmen und Datenstrukturen (ESE) Entwurf, Analyse und Umsetzung von Algorithmen (IEMS) WS 2014 / 2015 Vorlesung 14, Donnerstag, 5. Februar 2015 (Editierdistanz, dynamische Programmierung) Junior-Prof.
Algorithmen und Datenstrukturen (ESE) Entwurf, Analyse und Umsetzung von Algorithmen (IEMS) WS 2014 / 2015 Vorlesung 14, Donnerstag, 5. Februar 2015 (Editierdistanz, dynamische Programmierung) Junior-Prof.
Genomische Selektion in der Pflanzenzüchtung
 Genomische Selektion in der Pflanzenzüchtung Chris-CarolinCarolin Schön 30. März 2012 Hybridzüchtung Population 1 Population 2 Kreuzungen 10.000000 Linieni Prüfung 1 Umwelt Kreuzungen 10.000000 Linen 2.000
Genomische Selektion in der Pflanzenzüchtung Chris-CarolinCarolin Schön 30. März 2012 Hybridzüchtung Population 1 Population 2 Kreuzungen 10.000000 Linieni Prüfung 1 Umwelt Kreuzungen 10.000000 Linen 2.000
Zukunftsperspektiven in der Zuchtwertschätzung
 Zukunftsperspektiven in der Zuchtwertschätzung Dr. Stefan Rieder / Weiterbildungsveranstaltung des VSP / 8. November 2008 Fragen Was heisst genomischer Zuchtwert? Was heisst genomische Selektion? Wie kann
Zukunftsperspektiven in der Zuchtwertschätzung Dr. Stefan Rieder / Weiterbildungsveranstaltung des VSP / 8. November 2008 Fragen Was heisst genomischer Zuchtwert? Was heisst genomische Selektion? Wie kann
A3.1 Sortieralgorithmen
 Algorithmen und Datenstrukturen 1. März 2018 A3. : Selection- und Insertionsort Algorithmen und Datenstrukturen A3. : Selection- und Insertionsort Marcel Lüthi and Gabriele Röger Universität Basel 1. März
Algorithmen und Datenstrukturen 1. März 2018 A3. : Selection- und Insertionsort Algorithmen und Datenstrukturen A3. : Selection- und Insertionsort Marcel Lüthi and Gabriele Röger Universität Basel 1. März
Lehrstuhlvorstellung Molekularbiologie und Biochemie Botanisches Institut
 Lehrstuhlvorstellung Molekularbiologie und Biochemie Botanisches Institut 1 Holger Puchta Vorstellung Lehrstuhl Molekuarbiologie und Biochemie der Pflanzen SS 2017 Was machen wir? Wir machen keine Pflanzenphysiologie
Lehrstuhlvorstellung Molekularbiologie und Biochemie Botanisches Institut 1 Holger Puchta Vorstellung Lehrstuhl Molekuarbiologie und Biochemie der Pflanzen SS 2017 Was machen wir? Wir machen keine Pflanzenphysiologie
Programmierung 2 Studiengang MI / WI
 Programmierung 2 Studiengang MI / WI Dipl.-Inf., Dipl.-Ing. (FH) Michael Wilhelm Hochschule Harz FB Automatisierung und Informatik mwilhelm@hs-harz.de Raum 2.202 Tel. 03943 / 659 338 Fachbereich Automatisierung
Programmierung 2 Studiengang MI / WI Dipl.-Inf., Dipl.-Ing. (FH) Michael Wilhelm Hochschule Harz FB Automatisierung und Informatik mwilhelm@hs-harz.de Raum 2.202 Tel. 03943 / 659 338 Fachbereich Automatisierung
Einführung in die Informatik I Kapitel II.3: Sortieren
 1 Einführung in die Informatik I Kapitel II.3: Sortieren Prof. Dr.-Ing. Marcin Grzegorzek Juniorprofessur für Mustererkennung im Institut für Bildinformatik Department Elektrotechnik und Informatik Fakultät
1 Einführung in die Informatik I Kapitel II.3: Sortieren Prof. Dr.-Ing. Marcin Grzegorzek Juniorprofessur für Mustererkennung im Institut für Bildinformatik Department Elektrotechnik und Informatik Fakultät
Kapitel 3: Sortierverfahren Gliederung
 Gliederung 1. Grundlagen 2. Zahlentheoretische Algorithmen 3. Sortierverfahren 4. Ausgewählte Datenstrukturen 5. Dynamisches Programmieren 6. Graphalgorithmen 7. String-Matching 8. Kombinatorische Algorithmen
Gliederung 1. Grundlagen 2. Zahlentheoretische Algorithmen 3. Sortierverfahren 4. Ausgewählte Datenstrukturen 5. Dynamisches Programmieren 6. Graphalgorithmen 7. String-Matching 8. Kombinatorische Algorithmen
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 7 (11.07-15.07.) Methoden und Techniken II 1. Sie bekommen
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 7 (11.07-15.07.) Methoden und Techniken II 1. Sie bekommen
B / B* - Bäume. Guido Hildebrandt Seminar Datenbanksysteme
 B / B* - Bäume Guido Hildebrandt Seminar Datenbanksysteme 25.11.2010 Gliederung Einleitung Binärbaum B - Baum B* - Baum Varianten Zusammenfassung Quellen Gliederung Einleitung Binärbaum B - Baum B* - Baum
B / B* - Bäume Guido Hildebrandt Seminar Datenbanksysteme 25.11.2010 Gliederung Einleitung Binärbaum B - Baum B* - Baum Varianten Zusammenfassung Quellen Gliederung Einleitung Binärbaum B - Baum B* - Baum
