Strukturentstehung und -änderung bei Faltung und Funktion von
|
|
|
- Catrin Kopp
- vor 7 Jahren
- Abrufe
Transkript
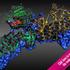
1 Strukturentstehung und -änderung bei Faltung und Funktion von Structural changes during protein folding and function Weikl, Thomas Max-Planck-Institut für Kolloid- und Grenzflächenforschung, Potsdam-Golm Korrespondierender Autor Zusammenfassung Die Sequenz eines Proteins bestimmt, in welche dreidimensionale Struktur es faltet. Die Struktur des Proteins wiederum ermöglicht seine biologische Funktion. Bei vielen erfordert die Ausübung dieser Funktion dynamische Änderungen und Anpassungen der dreidimensionalen Struktur. Die funktionsbedingten Strukturänderungen des Proteins und die Strukturentstehung bei der Faltung können experimentell nicht direkt beobachtet werden. Im Zusammenspiel mit theoretischen Modellierungen ermöglichen Mutationen eines Proteins jedoch einen indirekten Zugang zu diesen dynamischen Prozessen. Summary The sequence of a protein determines, in which three-dimensional structure it folds. The structure in turn enables the biological function of the protein. During function, many proteins slightly change and adapt their three-dimensional structures. These structural changes, as well as the structure formation during folding, cannot be observed directly in experiments. However, combined with theoretical modeling, mutations of a protein provide indirect access to these dynamic processes. Struktur und Funktion von Proteine sind Kettenmoleküle, die aus einzelnen Aminosäuren aufgebaut sind. Die genaue Sequenz der 20 verschiedenartigen Aminosäuren innerhalb der Proteinkette bestimmt dabei, in welche spezielle Struktur sich ein Protein faltet [1] (Abb. 1). Die dreidimensionale Struktur bestimmt wiederum die Funktionen der Proteine, die von der mechanischen Stabilisierung von Zellen und Geweben über die Katalyse von chemischen Reaktionen bis zum Transport von Molekülen reichen. Doch nur korrekt gefaltet kann ein Protein seine Funktion erfüllen. Fehler bei der Faltung können zu Proteinzuständen führen, die schwere Krankheiten wie Alzheimer, Parkinson oder das Creutzfeldt-Jakob-Syndrom hervorrufen Max-Planck-Gesellschaft 1/6
2 Die Struktur des Proteins CI2 besteht aus einer α-helix und einem β-faltblatt. Der Übergangszustand der Faltung Viele kleine Proteine falten ohne experimentell nachweisbare metastabile Zwischenzustände. Der erstaunlich direkte Übergang dieser Proteine vom ungefalteten in den gefalteten Zustand wird als Zwei-Zustands- Faltung bezeichnet. Entscheidend für die Faltungsdynamik dieser Proteine ist der Übergangszustand zwischen dem ungefalteten und dem gefalteten Zustand. Da dieser Übergangszustand als instabiler Zustand extrem kurzlebig ist, kann er nicht direkt beobachtet werden. Einen indirekten Zugang ermöglichen jedoch Mutationen eines Proteins, bei denen einzelne Aminosäuren ausgetauscht werden. Die Mutationen verändern geringfügig die Übergangszustandsbarriere und damit die Faltungs- und Entfaltungszeiten des Proteins [2]. Die zentrale Frage ist nun, wie sich der Übergangszustand aus den beobachteten Änderungen der Faltungszeit rekonstruieren lässt. In den letzten Jahren wurde ein neues Modell zur Rekonstruktion von Übergangszuständen aus Mutationsdaten entwickelt [3-5]. In diesem Modell wird der Übergangszustand als ein Ensemble von Übergangsstrukturen beschrieben. Eine zentrale Annahme des Modells ist, dass kooperative Strukturelemente wie α-helizes und β-haarnadeln in den einzelnen Übergangsstrukturen entweder vollständig gefaltet oder ungefaltet sind. In dem Modell werden zudem mutationsinduzierte Veränderungen der freien Energie in Komponenten für die Strukturelemente des Proteins aufgeteilt. Die Modellierung der experimentellen Daten verrät, in welchem Grad α-helizes and β-haarnadeln im Übergangszustand strukturiert sind. Im Falle der α- Helix des in Abbildung 1 gezeigten Proteins CI2 beispielsweise führt die Modellierung zu dem Ergebnis, dass die Helix im Übergangszustand vollständig ausgebildet, jedoch noch nicht an das β-faltblatt angelagert ist [4]. Schleifenschließung und Faltungswege Die überwiegende Mehrheit der Zwei-Zustands-Proteine hat eine Kettenlänge zwischen 60 und Max-Planck-Gesellschaft 2/6
3 Aminosäuren. Doch trotz ähnlicher Länge können sich die Faltungszeiten von Zwei-Zustands- um viele Größenordnungen unterscheiden. Die schnellsten Zwei-Zustands-Proteine falten innerhalb von Mikrosekunden, während die langsamsten mehrere Sekunden zur Faltung benötigen. Vor einigen Jahren wurde entdeckt, dass sich diese großen Unterschiede in den Faltungszeiten auf Unterschiede in den Proteinstrukturen zurückführen lassen [6]. Schnell faltende Proteine haben Strukturen mit überwiegend lokalen Kontakten zwischen den Aminosäuren. Bei einem lokalen Kontakt zwischen zwei Aminosäuren i und j ist der Sequenzabstand i-j der Aminosäuren klein. Im Gegensatz dazu weisen die Strukturen langsam faltender Proteine viele nichtlokale Kontakte mit großem Sequenzabstand auf. Nichtlokale Kontakte können im ungefalteten Zustand nur durch Schließen langer Schleifen in der Proteinkette gebildet werden, während bei lokalen Kontakten nur kurze Schleifen geschlossen werden müssen. Da kurze Schleifen schneller schließen als lange Schleifen, scheinen Schleifenschließungsereignisse für die unterschiedlichen Faltungszeiten verantwortlich zu sein [7]. Auch die Faltungswege dieser Proteine lassen sich aus Schleifenschießungsereignissen ableiten [7-9]. Der Faltungsweg eines Proteins ist durch die Reihenfolge bestimmt, in der die Kontakte zwischen den Aminosäuren gebildet werden. Dabei ist zu beachten, dass durch das Schließen von Kontakten Querverbindungen in der Proteinkette entstehen, die die Schleifenlängen bei der Bildung weiterer Kontakte verkürzen (Abb. 2). Ausschnitt einer Proteinkette m it bereits gebildetem Kontakt C 1 zwischen den Am inosäuren k und l. Die Querverbindung der Proteinkette durch C 1 verkürzt die Länge der Schleife, die zur Bildung des Kontakts C 2 zwischen den Am inosäuren i und j geschlossen werden m uss (rote Schleife). Ohne den Kontakt C 1 wäre die Schleife bei der Bildung des Kontakts C 2 deutlich länger (blaue Schleife). Es zeigt sich, dass Proteine wie ein dreidimensionaler Reißverschluss durch sukzessives Schließen kurzer Schleifen falten können. Auf diesen Faltungswegen bilden sich die Strukturelemente eines Proteins in charakteristischen Reihenfolgen (Abb. 3), aus denen sich häufig auch die grobe Struktur von Übergangszuständen ableiten lassen [7, 9] Max-Planck-Gesellschaft 3/6
4 Faltung des Proteins CI2 (s. Abb. 1) durch sukzessives Schließen kurzer Schleifen. Auf diesem Faltungsweg werden zunächst die α-helix und die β-strangverbindungen β 2 β 3 und β 3 β 4 gebildet, in beliebiger Reihenfolge. Diese drei Strukturelem ente verkürzen die Schleife, die dann bei der Bildung der Strangverbindung β 1 β 4 zwischen den beiden den geschlossen werden m uss. Strukturänderungen bei der Bindung von D ie biologische Funktion vieler Proteine erfordert kleinere oder größere Strukturänderungen im gefalteten Zustand. Solche Strukturänderungen können beispielsweise beim Binden von an andere Proteine oder kleinere Moleküle auftreten. Das belegen experimentell bestimmte Strukturen von in gebundenen und ungebundenen Zuständen. Wie die Strukturänderungen genau vonstatten gehen, ist jedoch experimentell nicht direkt beobachtbar. Bereits vor etwa 50 Jahren wurde vorgeschlagen, dass der Bindungspartner eines Proteins, der sogenannte Ligand, durch das Anbinden die Strukturänderung induziert (induced fit). Im Gegensatz dazu wurde vor einigen Jahren postuliert, dass Proteine bereits im ungebundenen Zustand verschiedene Strukturen durchlaufen, und der Ligand lediglich die passende Struktur wählt und durch das Anbinden stabilisiert (selected fit). Diese beiden Bindungswege lassen sich in einem einfachen Modell mit vier Zuständen veranschaulichen (Abb. 4). In diesem Modell kann das Protein zwei Strukturen P 1 und P 2 annehmen. Ohne Ligand hat das Protein im Grundzustand die Struktur P 1, und in einem angeregten Zustand die Struktur P 2. Mit gebundenem Liganden hingegen nimmt das Protein im Grundzustand P 2 L die Struktur P 2 an. Die beiden Grundzustände sind durch zwei verschiedene Bindungswege miteinander verbunden. Auf dem induced-fit-bindungsweg bindet das Protein den Liganden zunächst im Grundzustand P 1. Auf dem selected-fit-bindungsweg hingegen bindet der Ligand im angeregten Zustand P 2. Die Berechnung der Bindungskinetik in diesem Modell zeigt nun, dass nur die Bindungsrate des selected-fit-weges von der Energiedifferenz zwischen Grundzustand P 1 und angeregtem Zustand P 2 abhängt [10]. Mit Mutationen des Proteins, die diese Energiedifferenz beeinflussen, sollte sich deshalb unterscheiden lassen, ob ein Protein einen Liganden per induced fit oder per selected fit bindet Max-Planck-Gesellschaft 4/6
5 Einfaches Bindungsm odell eines Proteins m it zwei Strukturen. Auf dem induced-fit-bindungsweg bindet das Protein den Liganden im Grundzustand P 1. Auf dem selected-fit- Bindungsweg hingegen bindet das Protein den Liganden im angeregten Zustand P 2. Beide Bindungswege führen in den Grundzustand P 2 L des Protein-Liganden-Kom plexes. Originalveröffentlichungen Nach Erweiterungen suchenbilderweiterungchanneltickerdateilistehtml- ErweiterungJobtickerKalendererweiterungLinkerweiterungMPG.PuRe-ReferenzMitarbeiter (Employee Editor)PersonenerweiterungPublikationserweiterungTeaser mit BildTextblockerweiterungVeranstaltungstickererweiterungVideoerweiterungVideolistenerweiterungYouTube- Erweiterung [1] K. A. Dill, S. B. Ozkan, M. S. Shell, T. R. Weikl: The protein folding problem. Annual Review of Biophysics 37, (2008). [2] A. R. Fersht: Structure and mechanism in protein science. Freeman, New York 1999, 631 p. [3] C. Merlo, K. A. Dill, T. R. Weikl: Φ-values in protein folding kinetics have energetic and structural components. Proceedings of the National Academy of Sciences USA 102, (2005) Max-Planck-Gesellschaft 5/6
6 [4] T. R. Weikl, K. A. Dill: Transition states in protein folding kinetics: The structural interpretation of Φ-values. Journal of Molecular Biology 365, (2007). [5] T. R. Weikl: Transition states in protein folding kinetics: Modeling Φ-values of small β-sheet proteins. Biophysical Journal 94, (2008). [6] K. W. Plaxco, K. T. Simons, D. Baker: Contact order, transition state placement and the refolding rates of single domain proteins. Journal of Molecular Biology 277, (1998). [7] T. R. Weikl: Loop-closure principles in protein folding. Archives of Biochemistry and Biophysics 469, (2008). [8] T. R. Weikl, K. A. Dill: Folding rates and low-entropy-loss routes of two-state proteins. Journal of Molecular Biology 329, (2003). [9] T. R. Weikl: Loop-closure events during protein folding: Rationalizing the shape of Φ-value distributions. Proteins 60, (2005). [10] T. R. Weikl, C. von Deuster: Selected-fit versus induced-fit protein binding: Kinetic differences and mutational analysis. Proteins 75, (2009) Max-Planck-Gesellschaft 6/6
Studying Invisible Excited Protein States in Slow Exchange with a Major State Conformation
 Studying Invisible Excited Protein States in Slow Exchange with a Major State Conformation JACS 2012 Pramodh Vallurupalli, Guillaume Bouvignies, and Lewis E. Kay MR-Seminar Nina Kubatova 1 13.10.2014 Inhaltverzeichnis
Studying Invisible Excited Protein States in Slow Exchange with a Major State Conformation JACS 2012 Pramodh Vallurupalli, Guillaume Bouvignies, and Lewis E. Kay MR-Seminar Nina Kubatova 1 13.10.2014 Inhaltverzeichnis
Elektronenmikroskopie zeigte die Existenz der A-, P- und E- trna-bindungsstellen. Abb. aus Stryer (5th Ed.)
 Elektronenmikroskopie zeigte die Existenz der A-, P- und E- trna-bindungsstellen Die verschiedenen Ribosomen-Komplexe können im Elektronenmikroskop beobachtet werden Durch Röntgenkristallographie wurden
Elektronenmikroskopie zeigte die Existenz der A-, P- und E- trna-bindungsstellen Die verschiedenen Ribosomen-Komplexe können im Elektronenmikroskop beobachtet werden Durch Röntgenkristallographie wurden
Vertiefendes Seminar zur Vorlesung Biochemie I Bearbeitung Übungsblatt 4
 Vertiefendes Seminar zur Vorlesung Biochemie I 20.11.2015 Bearbeitung Übungsblatt 4 Gerhild van Echten-Deckert Fon. +49-228-732703 Homepage: http://www.limes-institut-bonn.de/forschung/arbeitsgruppen/unit-3/
Vertiefendes Seminar zur Vorlesung Biochemie I 20.11.2015 Bearbeitung Übungsblatt 4 Gerhild van Echten-Deckert Fon. +49-228-732703 Homepage: http://www.limes-institut-bonn.de/forschung/arbeitsgruppen/unit-3/
Falschfaltung von Proteinen
 Falschfaltung von Proteinen - Aggregation - domain swapping - amyloidogene Strukturen Was determiniert die Faltung von Proteinen? Einfachstes System: Zwei-Zustandsmodell N U Energie U dg ÜS dg* N Molekulare
Falschfaltung von Proteinen - Aggregation - domain swapping - amyloidogene Strukturen Was determiniert die Faltung von Proteinen? Einfachstes System: Zwei-Zustandsmodell N U Energie U dg ÜS dg* N Molekulare
Der schnellste Pfad der Evolution The fastest path of evolution
 Der schnellste Pfad der Evolution The fastest path of evolution Traulsen, Arne Max-Planck-Institut für Evolutionsbiologie, Plön Korrespondierender Autor E-Mail: traulsen@mpil-ploen.mpg.de Zusammenfassung
Der schnellste Pfad der Evolution The fastest path of evolution Traulsen, Arne Max-Planck-Institut für Evolutionsbiologie, Plön Korrespondierender Autor E-Mail: traulsen@mpil-ploen.mpg.de Zusammenfassung
Research Collection. Doctoral Thesis. ETH Library. Author(s): Greber, Basil Johannes. Publication Date: 2013
 Research Collection Doctoral Thesis Cryo-electron microscopy structures of large ribosomal subunit complexes insights into biogenesis, evolution, and regulation of the ribosome Author(s): Greber, Basil
Research Collection Doctoral Thesis Cryo-electron microscopy structures of large ribosomal subunit complexes insights into biogenesis, evolution, and regulation of the ribosome Author(s): Greber, Basil
Transkription und Translation sind in Eukaryoten räumlich und zeitlich getrennt. Abb. aus Stryer (5th Ed.)
 Transkription und Translation sind in Eukaryoten räumlich und zeitlich getrennt Die Initiation der Translation bei Eukaryoten Der eukaryotische Initiationskomplex erkennt zuerst das 5 -cap der mrna und
Transkription und Translation sind in Eukaryoten räumlich und zeitlich getrennt Die Initiation der Translation bei Eukaryoten Der eukaryotische Initiationskomplex erkennt zuerst das 5 -cap der mrna und
Einführung in die Biophysik
 Einführung in die Biophysik Quellen Schünemann: Biophysik Cotterill: Biophysik www.biophysics.org www.biophysj.org Sackmann: Lehrbuch der Biophysik Versuch einer Annäherung Biophysics is that branch of
Einführung in die Biophysik Quellen Schünemann: Biophysik Cotterill: Biophysik www.biophysics.org www.biophysj.org Sackmann: Lehrbuch der Biophysik Versuch einer Annäherung Biophysics is that branch of
Einführung in die Biophysik
 Einführung in die Biophysik Quellen Schünemann: Biophysik Cotterill: Biophysik www.biophysics.org www.biophysj.org Sackmann: Lehrbuch der Biophysik Versuch einer Annäherung Biophysics is that branch of
Einführung in die Biophysik Quellen Schünemann: Biophysik Cotterill: Biophysik www.biophysics.org www.biophysj.org Sackmann: Lehrbuch der Biophysik Versuch einer Annäherung Biophysics is that branch of
Mechanismen der Evolution als Matrize für Protein Engineering Evolutionary mechanisms as a template for protein engineering
 Mechanismen der Evolution als Matrize für Protein Engineering Evolutionary mechanisms as a template for protein engineering Höcker, Birte Max-Planck-Institut für Entwicklungsbiologie, Tübingen Korrespondierender
Mechanismen der Evolution als Matrize für Protein Engineering Evolutionary mechanisms as a template for protein engineering Höcker, Birte Max-Planck-Institut für Entwicklungsbiologie, Tübingen Korrespondierender
Die Rolle der Antwortmodalität beim Wechseln zwischen Aufgaben The role of response modalities in task switching
 Die Rolle der Antwortmodalität beim Wechseln zwischen The role of response modalities in task switching Philipp, Andrea M.; Koch, Iring Max-Planck-Institut für Kognitions- und Neurowissenschaften, Leipzig
Die Rolle der Antwortmodalität beim Wechseln zwischen The role of response modalities in task switching Philipp, Andrea M.; Koch, Iring Max-Planck-Institut für Kognitions- und Neurowissenschaften, Leipzig
Vertiefendes Seminar zur Vorlesung Biochemie
 Vertiefendes Seminar zur Vorlesung Biochemie 31.10.2014 Proteine: Struktur Gerhild van Echten-Deckert Fon. +49-228-732703 Homepage: http://www.limes-institut-bonn.de/forschung/arbeitsgruppen/unit-3/abteilung-van-echten-deckert/abt-van-echten-deckert-startseite/
Vertiefendes Seminar zur Vorlesung Biochemie 31.10.2014 Proteine: Struktur Gerhild van Echten-Deckert Fon. +49-228-732703 Homepage: http://www.limes-institut-bonn.de/forschung/arbeitsgruppen/unit-3/abteilung-van-echten-deckert/abt-van-echten-deckert-startseite/
Proteinfaltungen enthüllen den Ursprung des Lebens
 Powered by Seiten-Adresse: https://www.gesundheitsindustriebw.de/de/fachbeitrag/aktuell/proteinfaltungen-enthuellenden-ursprung-des-lebens/ Proteinfaltungen enthüllen den Ursprung des Lebens Computeranalysen
Powered by Seiten-Adresse: https://www.gesundheitsindustriebw.de/de/fachbeitrag/aktuell/proteinfaltungen-enthuellenden-ursprung-des-lebens/ Proteinfaltungen enthüllen den Ursprung des Lebens Computeranalysen
Darstellung und Charakterisierung zweier Modifikationen von (CuI) 2 (µ 2-2-Ethylpyrazin-N,N )
 Versuch F3 Darstellung und Charakterisierung zweier Modifikationen von (CuI) 2 (µ 2-2-Ethylpyrazin-N,N ) Einführung Der Begriff Polymorphie bezeichnet die Eigenschaft chemischer Verbindung in mehreren
Versuch F3 Darstellung und Charakterisierung zweier Modifikationen von (CuI) 2 (µ 2-2-Ethylpyrazin-N,N ) Einführung Der Begriff Polymorphie bezeichnet die Eigenschaft chemischer Verbindung in mehreren
Curriculum Vitae Prof. Dr. Martin Gruebele
 Curriculum Vitae Prof. Dr. Martin Gruebele Name: Martin Gruebele Geboren: 10. Januar 1964 Forschungsschwerpunkte: Protein und RNA Faltung, molekularer Energiefluss, Laser Rastertunnelmikroskopie von Glasen
Curriculum Vitae Prof. Dr. Martin Gruebele Name: Martin Gruebele Geboren: 10. Januar 1964 Forschungsschwerpunkte: Protein und RNA Faltung, molekularer Energiefluss, Laser Rastertunnelmikroskopie von Glasen
Zur Evolution technischer und biologischer Systeme Impulsvortrag
 Zur Evolution technischer und biologischer Systeme Impulsvortrag 12. Interdisziplinäres Gespräch Nachhaltigkeit und Technische Ökosysteme Leipzig, 2. Februar 2018 Justus Schollmeyer Robert Cummins, Functional
Zur Evolution technischer und biologischer Systeme Impulsvortrag 12. Interdisziplinäres Gespräch Nachhaltigkeit und Technische Ökosysteme Leipzig, 2. Februar 2018 Justus Schollmeyer Robert Cummins, Functional
Mechanismus der Enzymkatalyse
 Mechanismus der Enzymkatalyse Allgemeine Prinzipien Annäherung des Substrats an das aktive Zentrum des Enzyms Enzym und Substrat treten in Wechselwirkung: Bildung des [ES]-Komplexes. Konformationsänderung
Mechanismus der Enzymkatalyse Allgemeine Prinzipien Annäherung des Substrats an das aktive Zentrum des Enzyms Enzym und Substrat treten in Wechselwirkung: Bildung des [ES]-Komplexes. Konformationsänderung
Cluster-Struktur in Kernen. Cluster: Aus mehr als einem Nukleon zusammengesetzten und identifizierbarem Subsystem
 Cluster-Struktur in Kernen Cluster: Aus mehr als einem Nukleon zusammengesetzten und identifizierbarem Subsystem Die Struktur von 11 Li Beim Aufbruch von 11 Li wird nicht nur ein Neutron herausgeschlagen
Cluster-Struktur in Kernen Cluster: Aus mehr als einem Nukleon zusammengesetzten und identifizierbarem Subsystem Die Struktur von 11 Li Beim Aufbruch von 11 Li wird nicht nur ein Neutron herausgeschlagen
Untersuchung von Bindungsstellen zur Aktivierung von Genen Analysis of binding sites for the activation of genes
 Untersuchung von Bindungsstellen zur Aktivierung von Genen Analysis of binding sites for the activation of genes Vingron, Martin Max-Planck-Institut für molekulare Genetik, Berlin Korrespondierender Autor
Untersuchung von Bindungsstellen zur Aktivierung von Genen Analysis of binding sites for the activation of genes Vingron, Martin Max-Planck-Institut für molekulare Genetik, Berlin Korrespondierender Autor
Eukaryontische DNA-Bindedomänen
 1. Viele eukaryotische (und auch prokaryotische) Transkriptionsfaktoren besitzen eine DNA-bindende Domäne, die an eine ganz bestimmte DNA- Sequenz binden kann. Aufgrund von Ähnlichkeiten in der Struktur
1. Viele eukaryotische (und auch prokaryotische) Transkriptionsfaktoren besitzen eine DNA-bindende Domäne, die an eine ganz bestimmte DNA- Sequenz binden kann. Aufgrund von Ähnlichkeiten in der Struktur
2. Tertiärstruktur. Lernziele: 1) Verstehen wie Röntgenstrukturanalyse und NMR Spektroskopie gebraucht werden um Proteinstrukturen zu bestimmen.
 2. Tertiärstruktur Lernziele: 1) Verstehen wie Röntgenstrukturanalyse und NMR Spektroskopie gebraucht werden um Proteinstrukturen zu bestimmen. 2) Verstehen warum nicht polare Reste im inneren eines Proteins
2. Tertiärstruktur Lernziele: 1) Verstehen wie Röntgenstrukturanalyse und NMR Spektroskopie gebraucht werden um Proteinstrukturen zu bestimmen. 2) Verstehen warum nicht polare Reste im inneren eines Proteins
Die Persistenzlänge ist sequenzabhängig, für Poly-Serin etwa 5 AS. Der entfaltete Zustand ist Gegenstand intensiver Untersuchungen
 Die Bildung von Quartärstruktur ermöglicht den Bau großer, aber auch multifunktionaler Proteine 9.2 Proteinfaltung Proteine können unter bestimmten Bedingungen denaturiert (entfaltet) werden, das heißt,
Die Bildung von Quartärstruktur ermöglicht den Bau großer, aber auch multifunktionaler Proteine 9.2 Proteinfaltung Proteine können unter bestimmten Bedingungen denaturiert (entfaltet) werden, das heißt,
5 Zusammenfassung und Ausblick
 5 Zusammenfassung und Ausblick Die Kopplung von sekundären- und primären Aminen an die freie α-carboxylgruppe von L-Glutaminsäure bildet den Zugang zu Monomeren, die zum Aufbau von γ- Peptiden genutzt
5 Zusammenfassung und Ausblick Die Kopplung von sekundären- und primären Aminen an die freie α-carboxylgruppe von L-Glutaminsäure bildet den Zugang zu Monomeren, die zum Aufbau von γ- Peptiden genutzt
Andrei Lupas - Fasziniert von der komplexen Welt der Proteine
 Powered by Seiten-Adresse: https://www.gesundheitsindustriebw.de/de/fachbeitrag/aktuell/andrei-lupas-fasziniert-vonder-komplexen-welt-der-proteine/ Andrei Lupas - Fasziniert von der komplexen Welt der
Powered by Seiten-Adresse: https://www.gesundheitsindustriebw.de/de/fachbeitrag/aktuell/andrei-lupas-fasziniert-vonder-komplexen-welt-der-proteine/ Andrei Lupas - Fasziniert von der komplexen Welt der
GARCH ; : GARCH GARCH
 * : GARCH GARCH GARCH ; ; : GARCH : F831 : A 2005 7 21 ( ) Hamilton (1989) Engel Hamilton (1990) Klaassen(2002) Bergman Hansson (2005) Bollen (2000) 2005 7 21 Wilfling (2009) : ; * : (08JC790089) (2009R0079)
* : GARCH GARCH GARCH ; ; : GARCH : F831 : A 2005 7 21 ( ) Hamilton (1989) Engel Hamilton (1990) Klaassen(2002) Bergman Hansson (2005) Bollen (2000) 2005 7 21 Wilfling (2009) : ; * : (08JC790089) (2009R0079)
Quick Guide Home Network Mode
 Quick Guide Home Network Mode English > 1 German > 3 About the Home Network Mode EN Tivizen Nano & iplug normally work on their own created networks (whose SSID starts with tivizentv or iplug ) in which
Quick Guide Home Network Mode English > 1 German > 3 About the Home Network Mode EN Tivizen Nano & iplug normally work on their own created networks (whose SSID starts with tivizentv or iplug ) in which
Intelligente Algorithmen zur Analyse zellulärer Spleißmechanismen Intelligent Algorithms for the Analysis of Cellular Splicing Mechanisms
 Intelligente Algorithmen zur Analyse zellulärer Spleißmechanismen Intelligent Algorithms for the Analysis of Cellular Splicing Mechanisms Rätsch, Gunnar Friedrich-Miescher-Laboratorium für biologische
Intelligente Algorithmen zur Analyse zellulärer Spleißmechanismen Intelligent Algorithms for the Analysis of Cellular Splicing Mechanisms Rätsch, Gunnar Friedrich-Miescher-Laboratorium für biologische
MM Proteinmodelling. Michael Meyer. Vorlesung XVII
 Proteinmodelling Vorlesung XVII Proteinstrukturen Es besteht ein sehr großer Bedarf an Proteinstrukturen: Die Kenntnis der 3D-Struktur hat große Vorteile für das Design neuer Wirkstoffe. Experimentelle
Proteinmodelling Vorlesung XVII Proteinstrukturen Es besteht ein sehr großer Bedarf an Proteinstrukturen: Die Kenntnis der 3D-Struktur hat große Vorteile für das Design neuer Wirkstoffe. Experimentelle
Das modifizierte abdominelle»advancement«zur Neuformung der Submammarfalte als Grundlage für die anatomiegerechte Brustrekonstruktion
 Das modifizierte abdominelle»advancement«zur Neuformung der Submammarfalte als Grundlage für die anatomiegerechte Brustrekonstruktion Ursula Tanzella, Sophia Bethge, B. D. Krapohl K. Ueberreiter Summary
Das modifizierte abdominelle»advancement«zur Neuformung der Submammarfalte als Grundlage für die anatomiegerechte Brustrekonstruktion Ursula Tanzella, Sophia Bethge, B. D. Krapohl K. Ueberreiter Summary
Expression; Inclusion bodies was nun. Inclusion bodies
 Expression; Inclusion bodies was nun Löslich, aber auch gefaltet? Inclusion bodies Intrazelluläre Aggregate von missgefaltetem Protein Bilden sich bei Expression, wenn Protein sich nicht richtig faltet.
Expression; Inclusion bodies was nun Löslich, aber auch gefaltet? Inclusion bodies Intrazelluläre Aggregate von missgefaltetem Protein Bilden sich bei Expression, wenn Protein sich nicht richtig faltet.
"Rundum-Service" für alternde Nervenzellen Aid system for aging nerve cells
 "Rundum-Service" für alternde Aid system for aging nerve cells Kramer, Edgar; Aron, Liviu; Schulz, Jörg; Klein, Rüdiger Max-Planck-Institut für Neurobiologie, Martinsried Korrespondierender Autor E-Mail:
"Rundum-Service" für alternde Aid system for aging nerve cells Kramer, Edgar; Aron, Liviu; Schulz, Jörg; Klein, Rüdiger Max-Planck-Institut für Neurobiologie, Martinsried Korrespondierender Autor E-Mail:
Aufbau und Konformation von Polypeptiden
 1 Aufbau und Konformation von Polypeptiden Peter Güntert, Sommersemester 2009 Hierarchie von Proteinstrukturen Primärstruktur: Aminosäuresequenz Sekundärstruktur: Helices, Faltblätter, Turns, Loops Tertiärstruktur:
1 Aufbau und Konformation von Polypeptiden Peter Güntert, Sommersemester 2009 Hierarchie von Proteinstrukturen Primärstruktur: Aminosäuresequenz Sekundärstruktur: Helices, Faltblätter, Turns, Loops Tertiärstruktur:
Simulation von Brownscher Dynamik und Assoziationsraten von PP-Komplexen. Alexander Baldauf Montag
 Simulation von Brownscher Dynamik und Assoziationsraten von PP-Komplexen Alexander Baldauf Montag 25.04.2005 Motivation Typen von Interaktionen Verschiedene Methoden zur Vorhersage Wie kommen die beiden
Simulation von Brownscher Dynamik und Assoziationsraten von PP-Komplexen Alexander Baldauf Montag 25.04.2005 Motivation Typen von Interaktionen Verschiedene Methoden zur Vorhersage Wie kommen die beiden
Genexpressionsregulation
 Genexpressionsregulation Genexpressionsregulation Different tissue types 1 2 3 4 5 6 7 8 Taken from Caron et al., 2001 Verschiedene Ebenen der Genexpressionsregulation Epigenetic mechanisms Transkriptionskontrolle
Genexpressionsregulation Genexpressionsregulation Different tissue types 1 2 3 4 5 6 7 8 Taken from Caron et al., 2001 Verschiedene Ebenen der Genexpressionsregulation Epigenetic mechanisms Transkriptionskontrolle
UAufgabe 12: (evolutiv konservierte Aminosäuren)
 UAufgabe 12: (evolutiv konservierte Aminosäuren) Aufgabenstellung Wählen Sie zur Darstellung evolutiv konservierter Aminosäure-Positionen in "1lla" eine ihnen sinnvoll erscheinende Anfärbung. Exportieren
UAufgabe 12: (evolutiv konservierte Aminosäuren) Aufgabenstellung Wählen Sie zur Darstellung evolutiv konservierter Aminosäure-Positionen in "1lla" eine ihnen sinnvoll erscheinende Anfärbung. Exportieren
Das Gehirn am Rande des Chaos The brain on the edge of chaos
 Das Gehirn am Rande des Chaos The brain on the edge of chaos, Anna; Herrmann, Michael J.; Geisel, Theo Max-Planck-Institut für Dynamik und Selbstorganisation, Göttingen Korrespondierender Autor E-Mail:
Das Gehirn am Rande des Chaos The brain on the edge of chaos, Anna; Herrmann, Michael J.; Geisel, Theo Max-Planck-Institut für Dynamik und Selbstorganisation, Göttingen Korrespondierender Autor E-Mail:
Primärstruktur. Wintersemester 2011/12. Peter Güntert
 Primärstruktur Wintersemester 2011/12 Peter Güntert Primärstruktur Beziehung Sequenz Struktur Proteinsequenzen, Sequenzdatenbanken Sequenzvergleich (sequence alignment) Sequenzidentität, Sequenzhomologie
Primärstruktur Wintersemester 2011/12 Peter Güntert Primärstruktur Beziehung Sequenz Struktur Proteinsequenzen, Sequenzdatenbanken Sequenzvergleich (sequence alignment) Sequenzidentität, Sequenzhomologie
und Reinstruktur Die Sekundärstruktur ist die Anordnung der Aminosäurenkette, wobei man in zwei Arten unterscheidet: o Faltblatt- oder β- Struktur
 Aufbau von Proteinen insbesondere unter Betrachtung der Primär-,, Sekundär-,, Tertiär-,, Quartär-,, Supersekundär- und Reinstruktur Primärstruktur Unter Primärstruktur versteht man in der Biochemie die
Aufbau von Proteinen insbesondere unter Betrachtung der Primär-,, Sekundär-,, Tertiär-,, Quartär-,, Supersekundär- und Reinstruktur Primärstruktur Unter Primärstruktur versteht man in der Biochemie die
Übungsaufgaben. Aufbau und Konformation von Polypeptiden. Einführung in die räumliche Struktur von Proteinen
 Computergestützte Strukturbiologie (Strukturelle Bioinformatik) SS09 P. Güntert Übungsaufgaben Aufbau und Konformation von Polypeptiden 1. Warum haben Proteine im Unterschied zu DNA komplizierte und vielfältige
Computergestützte Strukturbiologie (Strukturelle Bioinformatik) SS09 P. Güntert Übungsaufgaben Aufbau und Konformation von Polypeptiden 1. Warum haben Proteine im Unterschied zu DNA komplizierte und vielfältige
Aufgabe 5 (Supersekundärstruktur)
 Aufgabe 5 (Supersekundärstruktur) Fragestellung Bei der Untereinheit des Arthropodenhämocyanins aus Limulus polyphemus werden folgende Fragestellungen untersucht: - Welche Supersekundärstrukturen gibt
Aufgabe 5 (Supersekundärstruktur) Fragestellung Bei der Untereinheit des Arthropodenhämocyanins aus Limulus polyphemus werden folgende Fragestellungen untersucht: - Welche Supersekundärstrukturen gibt
Konfiguration von eduroam. Configuring eduroam
 eduroam Windows 8.1 / 10 Konfiguration von eduroam Configuring eduroam 08.10.2018 kim.uni-hohenheim.de kim@uni-hohenheim.de Wissenschaftliche Einrichtungen und Universitäten bieten einen weltweiten Internetzugang
eduroam Windows 8.1 / 10 Konfiguration von eduroam Configuring eduroam 08.10.2018 kim.uni-hohenheim.de kim@uni-hohenheim.de Wissenschaftliche Einrichtungen und Universitäten bieten einen weltweiten Internetzugang
LS Kopplung. = a ij l i l j. W li l j. = b ij s i s j. = c ii l i s i. W li s j J = L + S. L = l i L = L(L + 1) J = J(J + 1) S = s i S = S(S + 1)
 LS Kopplung in many electron systems there are many li and si the coupling to for total momentum J depends on the energetic ordering of the interactions orbital momenta interaction W li l j = a ij l i
LS Kopplung in many electron systems there are many li and si the coupling to for total momentum J depends on the energetic ordering of the interactions orbital momenta interaction W li l j = a ij l i
FOLDALIGN und sein Algorithmus. Nadine Boley Silke Szymczak
 FOLDALIGN und sein Algorithmus Nadine Boley Silke Szymczak Gliederung 2 Einleitung Motivation des Ansatzes zu FOLDALIGN Sankoff-Algorithmus Globales Alignment Zuker-Algorithmus Kombination FOLDALIGN Algorithmus,
FOLDALIGN und sein Algorithmus Nadine Boley Silke Szymczak Gliederung 2 Einleitung Motivation des Ansatzes zu FOLDALIGN Sankoff-Algorithmus Globales Alignment Zuker-Algorithmus Kombination FOLDALIGN Algorithmus,
Jürgen Baier (Autor) Untersuchung der Strukturdynamik einzelner Proteine bei tiefen Temperaturen
 Jürgen Baier (Autor) Untersuchung der Strukturdynamik einzelner Proteine bei tiefen Temperaturen https://cuvillier.de/de/shop/publications/6365 Copyright: Cuvillier Verlag, Inhaberin Annette Jentzsch-Cuvillier,
Jürgen Baier (Autor) Untersuchung der Strukturdynamik einzelner Proteine bei tiefen Temperaturen https://cuvillier.de/de/shop/publications/6365 Copyright: Cuvillier Verlag, Inhaberin Annette Jentzsch-Cuvillier,
VGM. VGM information. HAMBURG SÜD VGM WEB PORTAL USER GUIDE June 2016
 Overview The Hamburg Süd VGM Web portal is an application that enables you to submit VGM information directly to Hamburg Süd via our e-portal Web page. You can choose to enter VGM information directly,
Overview The Hamburg Süd VGM Web portal is an application that enables you to submit VGM information directly to Hamburg Süd via our e-portal Web page. You can choose to enter VGM information directly,
Reaktionskinetik. Maximilian Erlacher. Quelle: Mathematical Biology: I. An Introduction, Third Edition J.D. Murray Springer
 Reaktionskinetik Maximilian Erlacher Quelle: Mathematical Biology: I. An Introduction, Third Edition J.D. Murray Springer Themen: 1 Basisenzymreaktion 2 Michaelis-Menten-Analyse 3 Selbstauslöschende Kinetik
Reaktionskinetik Maximilian Erlacher Quelle: Mathematical Biology: I. An Introduction, Third Edition J.D. Murray Springer Themen: 1 Basisenzymreaktion 2 Michaelis-Menten-Analyse 3 Selbstauslöschende Kinetik
Proteinstrukturklassen α-helikale Proteine
 Proteinstrukturklassen α-helikale Proteine Wintersemester 2011/12 Peter Güntert Domäne Modul Faltung Domäne (domain): Polypeptidkette (oder Teil davon), die unabhängig in eine stabile, kompakte Tertiärstruktur
Proteinstrukturklassen α-helikale Proteine Wintersemester 2011/12 Peter Güntert Domäne Modul Faltung Domäne (domain): Polypeptidkette (oder Teil davon), die unabhängig in eine stabile, kompakte Tertiärstruktur
Thema heute: Aufbau der Materie: Das Bohr sche Atommodell
 Wiederholung der letzten Vorlesungsstunde: Erste Atommodelle, Dalton Thomson, Rutherford, Atombau, Coulomb-Gesetz, Proton, Elektron, Neutron, weitere Elementarteilchen, atomare Masseneinheit u, 118 bekannte
Wiederholung der letzten Vorlesungsstunde: Erste Atommodelle, Dalton Thomson, Rutherford, Atombau, Coulomb-Gesetz, Proton, Elektron, Neutron, weitere Elementarteilchen, atomare Masseneinheit u, 118 bekannte
1 Der Elektronentransfer: Theorie nach Marcus und Hush
 1 Der Elektronentransfer: Theorie nach Marcus und Hush Betrachtet wird der Elektronentransfer zwischen zwei solvatisierten Spezies in einer Lösung. Es gibt zwei Arten von Elektronentransfer, Reaktionen
1 Der Elektronentransfer: Theorie nach Marcus und Hush Betrachtet wird der Elektronentransfer zwischen zwei solvatisierten Spezies in einer Lösung. Es gibt zwei Arten von Elektronentransfer, Reaktionen
Das Zytoskelett. Intrazelluläre Mikrotubuliorganisation. Centrosomen. Mikrotubuli-bindende Proteine
 Das Zytoskelett Intrazelluläre Mikrotubuliorganisation Centrosomen Mikrotubuli-bindende Proteine Filamente des Zytoskeletts halten Zellen in Form Tubulin Aktin DNA Mikrotubuliaufbau in doppel oder dreifach
Das Zytoskelett Intrazelluläre Mikrotubuliorganisation Centrosomen Mikrotubuli-bindende Proteine Filamente des Zytoskeletts halten Zellen in Form Tubulin Aktin DNA Mikrotubuliaufbau in doppel oder dreifach
Grundlagen der Molekularen Biophysik WS 2011/12 (Bachelor)
 Grundlagen der Molekularen Biophysik WS 2011/12 (Bachelor) Dozent: Prof Dr. Ulrike Alexiev (R.1.2.34, Tel. 55010/Sekretariat Frau Endrias Tel. 53337) Tutoren: Dr. Kristina Kirchberg Alex Boreham 6-stündig
Grundlagen der Molekularen Biophysik WS 2011/12 (Bachelor) Dozent: Prof Dr. Ulrike Alexiev (R.1.2.34, Tel. 55010/Sekretariat Frau Endrias Tel. 53337) Tutoren: Dr. Kristina Kirchberg Alex Boreham 6-stündig
Folding Funnel Rädler / Mathias 45 SS2011
 Folding Funnel 45 Proteinfaltung am Computer Snow/Pande: Folding at home Molekulardynamik Simulationen Integration Newtonscher Bewegungsgleichungen Kraftfeld für kovalente Bindungen Elektrostatische Wechselwirkungen,
Folding Funnel 45 Proteinfaltung am Computer Snow/Pande: Folding at home Molekulardynamik Simulationen Integration Newtonscher Bewegungsgleichungen Kraftfeld für kovalente Bindungen Elektrostatische Wechselwirkungen,
Universität Stuttgart Institut für Technische Biochemie Lehrstuhl für Biochemie
 Universität Stuttgart Institut für Technische Biochemie Lehrstuhl für Biochemie Address Pfaffenwaldring 55 70569 Stuttgart Deutschland Telephone +49 711 685-64391 Fax +49 711 685-64392 E-Mail elisabeth.tosta@ibc.uni-stuttgart.de
Universität Stuttgart Institut für Technische Biochemie Lehrstuhl für Biochemie Address Pfaffenwaldring 55 70569 Stuttgart Deutschland Telephone +49 711 685-64391 Fax +49 711 685-64392 E-Mail elisabeth.tosta@ibc.uni-stuttgart.de
Bioorganische Chemie Enzymatische Katalyse 2011
 Ringvorlesung Chemie B - Studiengang Molekulare Biotechnologie Bioorganische Chemie Enzymatische Katalyse 2011 Prof. Dr. A. Jäschke INF 364, Zi. 308, Tel. 54 48 51 jaeschke@uni-hd.de Lehrziele I Kenntnis
Ringvorlesung Chemie B - Studiengang Molekulare Biotechnologie Bioorganische Chemie Enzymatische Katalyse 2011 Prof. Dr. A. Jäschke INF 364, Zi. 308, Tel. 54 48 51 jaeschke@uni-hd.de Lehrziele I Kenntnis
Kapitel 5: Protein-Datendanken
 Kapitel 5: Protein-Datendanken Vom Gen zum Protein n Motivation und historische Entwicklung n Proteomics Datengewinnung PEDRo-Projekt n Protein-Datenbanken Anforderungen Sequenz-Datenbanken Domain/Familien-Datenbanken
Kapitel 5: Protein-Datendanken Vom Gen zum Protein n Motivation und historische Entwicklung n Proteomics Datengewinnung PEDRo-Projekt n Protein-Datenbanken Anforderungen Sequenz-Datenbanken Domain/Familien-Datenbanken
Zustände Zustandsdiagramme
 Zustände Zustandsdiagramme Ereignisse Zustandsübergänge Dr. Beatrice Amrhein Überblick Definition Anwendungsbereich Zustände/Zustandsübergänge Aktionen Ereignisse 2 Verwendung von Zuständen 3 Verwendung
Zustände Zustandsdiagramme Ereignisse Zustandsübergänge Dr. Beatrice Amrhein Überblick Definition Anwendungsbereich Zustände/Zustandsübergänge Aktionen Ereignisse 2 Verwendung von Zuständen 3 Verwendung
Enzyme SPF BCH am
 Enzyme Inhaltsverzeichnis Ihr kennt den Aufbau von Proteinen (mit vier Strukturelementen) und kennt die Kräfte, welche den Aufbau und die Funktion von Enzymen bestimmen... 3 Ihr versteht die Einteilung
Enzyme Inhaltsverzeichnis Ihr kennt den Aufbau von Proteinen (mit vier Strukturelementen) und kennt die Kräfte, welche den Aufbau und die Funktion von Enzymen bestimmen... 3 Ihr versteht die Einteilung
Transkription Teil 2. - Transkription bei Eukaryoten -
 Transkription Teil 2 - Transkription bei Eukaryoten - Inhalte: Unterschiede in der Transkription von Pro- und Eukaryoten Die RNA-Polymerasen der Eukaryoten Cis- und trans-aktive Elemente Promotoren Transkriptionsfaktoren
Transkription Teil 2 - Transkription bei Eukaryoten - Inhalte: Unterschiede in der Transkription von Pro- und Eukaryoten Die RNA-Polymerasen der Eukaryoten Cis- und trans-aktive Elemente Promotoren Transkriptionsfaktoren
Increased risk for flashback in case of dynamic operation of gas turbines
 Wir schaffen Wissen heute für morgen Increased risk for flashback in case of dynamic operation of gas turbines Yu-Chun Lin 28. August 2013 1 Introduction Pre-combustion CO 2 capture H 2 -rich fuel mixtures
Wir schaffen Wissen heute für morgen Increased risk for flashback in case of dynamic operation of gas turbines Yu-Chun Lin 28. August 2013 1 Introduction Pre-combustion CO 2 capture H 2 -rich fuel mixtures
Normalvalente & nicht-normalvalente* Verbindungen nur normalvalente Verbindungen
 Normalvalente & nicht-normalvalente* Verbindungen 1 B C N Ne nur normalvalente Verbindungen Al Ga In Tl i Ge n Pb P As b Bi e Te Po Cl Br I At Ar Kr Xe Rn normalvalente Verbindungen befolgen die (8-N)
Normalvalente & nicht-normalvalente* Verbindungen 1 B C N Ne nur normalvalente Verbindungen Al Ga In Tl i Ge n Pb P As b Bi e Te Po Cl Br I At Ar Kr Xe Rn normalvalente Verbindungen befolgen die (8-N)
Das Zytoskelett (Gastvorlesung R. Brandt, Neurobiologie)
 Das Zytoskelett (Gastvorlesung R. Brandt, Neurobiologie) Inhalt: 1. Struktur und Dynamik der zytoskeletalen Filamentsysteme 2. Regulation der zytoskeletalen Komponenten 3. Molekulare Motoren 4. Zytoskelett
Das Zytoskelett (Gastvorlesung R. Brandt, Neurobiologie) Inhalt: 1. Struktur und Dynamik der zytoskeletalen Filamentsysteme 2. Regulation der zytoskeletalen Komponenten 3. Molekulare Motoren 4. Zytoskelett
Chemie für Biologen WS 2005/6 Arne Lützen Institut für Organische Chemie der Universität Duisburg-Essen (Teil 5: )
 Chemie für Biologen WS 2005/6 Arne Lützen Institut für rganische Chemie der Universität Duisburg-Essen (Teil 5: 23.11.2005) Kovalente Bindung Atome können sich Valenzelektronen unter Ausbildung von Bindungen
Chemie für Biologen WS 2005/6 Arne Lützen Institut für rganische Chemie der Universität Duisburg-Essen (Teil 5: 23.11.2005) Kovalente Bindung Atome können sich Valenzelektronen unter Ausbildung von Bindungen
Neue Proteine zur Aktivierung molekularer Schalter in Pflanzen Novel proteins for the activation of molecular switches in plants
 Neue Proteine zur Aktivierung molekularer Schalter in Pflanzen Novel proteins for the activation of molecular switches in plants Berken, Antje; Fricke, Inka; Scrima, Andrea; Thomas, Christoph; Weyand,
Neue Proteine zur Aktivierung molekularer Schalter in Pflanzen Novel proteins for the activation of molecular switches in plants Berken, Antje; Fricke, Inka; Scrima, Andrea; Thomas, Christoph; Weyand,
Wie der Körper Sprache und Vorstellungsvermögen im Gehirn formt How the body shapes language and imagination in the brain
 Wie der Körper Sprache und Vorstellungsvermögen im Gehirn formt How the body shapes language and imagination in the brain Casasanto, Daniel Max-Planck-Institut für Psycholinguistik, Nijmegen, Netherlands
Wie der Körper Sprache und Vorstellungsvermögen im Gehirn formt How the body shapes language and imagination in the brain Casasanto, Daniel Max-Planck-Institut für Psycholinguistik, Nijmegen, Netherlands
Einblicke in die Regulation der Zellteilung New insights into cell cycle regulation
 Einblicke in die Regulation der Zellteilung New insights into cell cycle regulation Hauf, Silke Friedrich-Miescher-Laboratorium für biologische Arbeitsgruppen in der Max-Planck-Gesellschaft, Tübingen Korrespondierender
Einblicke in die Regulation der Zellteilung New insights into cell cycle regulation Hauf, Silke Friedrich-Miescher-Laboratorium für biologische Arbeitsgruppen in der Max-Planck-Gesellschaft, Tübingen Korrespondierender
THEORY OF MIND TEIL 2
 Seminar Vertiefung in Entwicklungspsychologie Dozentin: Susanne Kristen Wintersemester 2010/11 THEORY OF MIND TEIL 2 Nicole Biebel 6.12.2010 Gliederung 1) Theory of Mind ab 4 Jahren 1) Fähigkeiten mit
Seminar Vertiefung in Entwicklungspsychologie Dozentin: Susanne Kristen Wintersemester 2010/11 THEORY OF MIND TEIL 2 Nicole Biebel 6.12.2010 Gliederung 1) Theory of Mind ab 4 Jahren 1) Fähigkeiten mit
An Introduction to Monetary Theory. Rudolf Peto
 An Introduction to Monetary Theory Rudolf Peto 0 Copyright 2013 by Prof. Rudolf Peto, Bielefeld (Germany), www.peto-online.net 1 2 Preface This book is mainly a translation of the theoretical part of my
An Introduction to Monetary Theory Rudolf Peto 0 Copyright 2013 by Prof. Rudolf Peto, Bielefeld (Germany), www.peto-online.net 1 2 Preface This book is mainly a translation of the theoretical part of my
T-Zellen werden zur Kontrolle intrazellulärer Pathogene benötigt und um B Zellen gegen die meisten Antigene zu aktivieren
 Komponenten und Aufbau des Immunsystems bakterielle Toxine spezifische Antikörper Bakterien im extrazellulären Raum Bakterien im Plasma Antikörper können auf drei Arten an der Immunabwehr beteiligt sein
Komponenten und Aufbau des Immunsystems bakterielle Toxine spezifische Antikörper Bakterien im extrazellulären Raum Bakterien im Plasma Antikörper können auf drei Arten an der Immunabwehr beteiligt sein
Zusammenfassung. Summary
 Vorhersage von Materialeigenschaften auf dem Computer: Jüngste Erfolge quantenmechanischer Simulationsmethoden Computer-based prediction of materials properties: Recent achievements of quantum-mechanical
Vorhersage von Materialeigenschaften auf dem Computer: Jüngste Erfolge quantenmechanischer Simulationsmethoden Computer-based prediction of materials properties: Recent achievements of quantum-mechanical
VL Bioinformatik für Nebenfächler SS2018 Woche 1. Tim Conrad AG Medical Bioinformatics Institut für Mathematik & Informatik, Freie Universität Berlin
 VL Bioinformatik für Nebenfächler SS2018 Woche 1 Tim Conrad AG Medical Bioinformatics Institut für Mathematik & Informatik, Freie Universität Berlin Die Themen heute 1. Team 2. Tutorien 3. Prüfungsleistungen
VL Bioinformatik für Nebenfächler SS2018 Woche 1 Tim Conrad AG Medical Bioinformatics Institut für Mathematik & Informatik, Freie Universität Berlin Die Themen heute 1. Team 2. Tutorien 3. Prüfungsleistungen
Interaktionsnetzwerke in Proteinstrukturen Interaction networks in protein structures
 Interaktionsnetzwerke in Proteinstrukturen Interaction networks in protein structures Lappe, Michael Max-Planck-Institut für molekulare Genetik, Berlin Korrespondierender Autor E-Mail: lappe@molgen.mpg.de
Interaktionsnetzwerke in Proteinstrukturen Interaction networks in protein structures Lappe, Michael Max-Planck-Institut für molekulare Genetik, Berlin Korrespondierender Autor E-Mail: lappe@molgen.mpg.de
Wissenschaftliches Schreiben in der AC
 Wissenschaftliches Schreiben in der AC Saarbrücken, den 6 Publikationen in Wissenschaftlichen Zeitschriften > 1 Einleitung Inhalte der Übung Wissenschaftliches Schreiben in der AC 1 Einleitung 2 Wichtige
Wissenschaftliches Schreiben in der AC Saarbrücken, den 6 Publikationen in Wissenschaftlichen Zeitschriften > 1 Einleitung Inhalte der Übung Wissenschaftliches Schreiben in der AC 1 Einleitung 2 Wichtige
Vorlesung Allgemeine Chemie (CH01)
 Vorlesung Allgemeine Chemie (CH01) Für Studierende im B.Sc.-Studiengang Chemie Prof. Dr. Martin Köckerling Arbeitsgruppe Anorganische Festkörperchemie Mathematisch-Naturwissenschaftliche Fakultät, Institut
Vorlesung Allgemeine Chemie (CH01) Für Studierende im B.Sc.-Studiengang Chemie Prof. Dr. Martin Köckerling Arbeitsgruppe Anorganische Festkörperchemie Mathematisch-Naturwissenschaftliche Fakultät, Institut
Chemie für Biologen SS Georg Jansen AG Theoretische Organische Chemie Universität Duisburg Essen. (Teil 3: Kovalente Bindungen)
 Chemie für Biologen SS 2007 Georg Jansen AG Theoretische rganische Chemie Universität Duisburg Essen (Teil 3: Kovalente Bindungen) (3) Kovalente Bindung Atome können sich Valenzelektronen unter Ausbildung
Chemie für Biologen SS 2007 Georg Jansen AG Theoretische rganische Chemie Universität Duisburg Essen (Teil 3: Kovalente Bindungen) (3) Kovalente Bindung Atome können sich Valenzelektronen unter Ausbildung
Hinweisblatt. Für den Einsatz des MAX! Heizungssteuerungssystems haben Sie zwei Alternativen: Die MAX! Einzelraumlösung und die MAX! Hauslösung.
 Hinweisblatt MAX! Heizkörperthermostat BC-RT-TRX-CyG Art.-Nr. 99017 MAX! Fensterkontakt BC-SC-Rd-WM Art.-Nr. 99023 Für den Einsatz des MAX! Heizungssteuerungssystems haben Sie zwei Alternativen: Die MAX!
Hinweisblatt MAX! Heizkörperthermostat BC-RT-TRX-CyG Art.-Nr. 99017 MAX! Fensterkontakt BC-SC-Rd-WM Art.-Nr. 99023 Für den Einsatz des MAX! Heizungssteuerungssystems haben Sie zwei Alternativen: Die MAX!
Theorie der Proteinfaltung
 Theorie der Proteinfaltung Strukturelle Bioinformatik WS15/16 Dr. Stefan Simm, 09.12.2015 simm@bio.uni-frankfurt.de Proteinfaltung EINLEITUNG Proteinfaltung physikalischer Prozeß, mit dem ein Polypeptid
Theorie der Proteinfaltung Strukturelle Bioinformatik WS15/16 Dr. Stefan Simm, 09.12.2015 simm@bio.uni-frankfurt.de Proteinfaltung EINLEITUNG Proteinfaltung physikalischer Prozeß, mit dem ein Polypeptid
Alle Angaben sind ohne Gewähr!
 Alle Angaben sind ohne Gewähr! Die Abbildungen sind hauptsächlich aus dem Buch: Van Holde/Johnson/Ho: Principles of physical biochemistry Buch nur zur Kristallographie: Crystallography Made Crystal Clear:
Alle Angaben sind ohne Gewähr! Die Abbildungen sind hauptsächlich aus dem Buch: Van Holde/Johnson/Ho: Principles of physical biochemistry Buch nur zur Kristallographie: Crystallography Made Crystal Clear:
P As Sb. S Se Te. Si Ge Sn. Cl Br I. Al Ga In. Ar Kr Xe. Normalvalente & nicht-normalvalente* Verbindungen. Radioaktiv. nur normalvalente Verbindungen
 Normalvalente & nicht-normalvalente* Verbindungen 1 B C N Ne nur normalvalente Verbindungen Al Ga In Si Ge Sn P As Sb S Se Te Cl Br I Ar Kr Xe normalvalente Verbindungen befolgen die (8-N) Regel (N = Anzahl
Normalvalente & nicht-normalvalente* Verbindungen 1 B C N Ne nur normalvalente Verbindungen Al Ga In Si Ge Sn P As Sb S Se Te Cl Br I Ar Kr Xe normalvalente Verbindungen befolgen die (8-N) Regel (N = Anzahl
Theoretical Biophysics - Quantum Theory and Molecular Dynamics. 10. Vorlesung. Pawel Romanczuk WS 2016/17
 Theoretical Biophysics - Quantum Theory and Molecular Dynamics 10. Vorlesung Pawel Romanczuk WS 2016/17 http://lab.romanczuk.de/teaching Zusammenfassung letzte VL Der Spin Grundlegende Eigenschaften Spin
Theoretical Biophysics - Quantum Theory and Molecular Dynamics 10. Vorlesung Pawel Romanczuk WS 2016/17 http://lab.romanczuk.de/teaching Zusammenfassung letzte VL Der Spin Grundlegende Eigenschaften Spin
NEUE BEHANDLUNGSMÖGLICHKEITEN MONOKLONALE ANTIKÖRPER
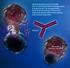 NEUE BEHANDLUNGSMÖGLICHKEITEN MONOKLONALE ANTIKÖRPER Was sind Antikörper? Antikörper patrouillieren wie Wächter im Blutkreislauf des Körpers und achten auf Krankheitserreger wie Bakterien, Viren und Parasiten
NEUE BEHANDLUNGSMÖGLICHKEITEN MONOKLONALE ANTIKÖRPER Was sind Antikörper? Antikörper patrouillieren wie Wächter im Blutkreislauf des Körpers und achten auf Krankheitserreger wie Bakterien, Viren und Parasiten
Einführung in die Linguistik, Teil 4
 Einführung in die Linguistik, Teil 4 Menschliche Sprachverarbeitung im Rahmen der Kognitionswissenschaft Markus Bader, Frans Plank, Henning Reetz, Björn Wiemer Einführung in die Linguistik, Teil 4 p. 1/19
Einführung in die Linguistik, Teil 4 Menschliche Sprachverarbeitung im Rahmen der Kognitionswissenschaft Markus Bader, Frans Plank, Henning Reetz, Björn Wiemer Einführung in die Linguistik, Teil 4 p. 1/19
Gene-Silencing in transgenen Pflanzen Gene silencing in transgenic plants
 Gene-Silencing in transgenen Pflanzen Gene silencing in transgenic plants Schmidt, Renate; Arlt, Matthias Max-Planck-Institut für molekulare Pflanzenphysiologie, Potsdam-Golm Korrespondierender Autor E-Mail:
Gene-Silencing in transgenen Pflanzen Gene silencing in transgenic plants Schmidt, Renate; Arlt, Matthias Max-Planck-Institut für molekulare Pflanzenphysiologie, Potsdam-Golm Korrespondierender Autor E-Mail:
Interest rate volatility prior to monetary union under alternative pre-switch regimes
 Interest rate volatility prior to monetary union under alternative pre-switch regimes Bernd Wilfling HWWA DISCUSSION PAPER 143 Hamburgisches Welt-Wirtschafts-Archiv (HWWA) Hamburg Institute of International
Interest rate volatility prior to monetary union under alternative pre-switch regimes Bernd Wilfling HWWA DISCUSSION PAPER 143 Hamburgisches Welt-Wirtschafts-Archiv (HWWA) Hamburg Institute of International
Three-Dimensional Free-Radical Polymerization
 Three-Dimensional Free-Radical Polymerization Cross-Linked and Hyper-Branched Polymers Bearbeitet von Gennady V Korolyov, Michael Mogilevich 1. Auflage 2009. Buch. xvi, 272 S. Hardcover ISBN 978 3 540
Three-Dimensional Free-Radical Polymerization Cross-Linked and Hyper-Branched Polymers Bearbeitet von Gennady V Korolyov, Michael Mogilevich 1. Auflage 2009. Buch. xvi, 272 S. Hardcover ISBN 978 3 540
Die Evolution der mrns-expression bei Mensch und Schimpanse The evolution of mrna expression in humans and chimpanzees
 Die Evolution der mrns-expression bei Mensch und Schimpanse The evolution of mrna expression in humans and chimpanzees Lachmann, Michael Max-Planck-Institut für evolutionäre Anthropologie, Leipzig Korrespondierender
Die Evolution der mrns-expression bei Mensch und Schimpanse The evolution of mrna expression in humans and chimpanzees Lachmann, Michael Max-Planck-Institut für evolutionäre Anthropologie, Leipzig Korrespondierender
Jahrbuch 2008/2009 Arndt, Peter F. Die Kopplung zellulärer und mutagener Prozesse bei der Evolution von Säugetieren
 Die Kopplung zellulärer und mutagener Prozesse bei der Evolution von The interconnection of mutagenic and cellular processes during the evolution of mammals Arndt, Peter F. Max-Planck-Institut für molekulare
Die Kopplung zellulärer und mutagener Prozesse bei der Evolution von The interconnection of mutagenic and cellular processes during the evolution of mammals Arndt, Peter F. Max-Planck-Institut für molekulare
Einführung in die Biochemie Wirkungsweise von Enzymen
 Wirkungsweise von en Am Aktiven Zentrum kann ein nur in einer ganz bestimmten Orientierung anlegen, wie ein Schlüssel zum Schloss. Dieses Prinzip ist die Ursache der spezifität von en. Dies resultiert
Wirkungsweise von en Am Aktiven Zentrum kann ein nur in einer ganz bestimmten Orientierung anlegen, wie ein Schlüssel zum Schloss. Dieses Prinzip ist die Ursache der spezifität von en. Dies resultiert
Molecular Dynamics of Proteorhodopsin in Lipid Bilayers by Solid-State NMR
 Molecular Dynamics of Proteorhodopsin in Lipid Bilayers by Solid-State NMR Yang, Aslimovsk, Glaubitz Moderne Anwendungen der Magnetischen Resonanz Lena Kalinowsky Motivation/Ziel Temperatur Hydrathülle
Molecular Dynamics of Proteorhodopsin in Lipid Bilayers by Solid-State NMR Yang, Aslimovsk, Glaubitz Moderne Anwendungen der Magnetischen Resonanz Lena Kalinowsky Motivation/Ziel Temperatur Hydrathülle
Thema heute: Das Bohr sche Atommodell
 Wiederholung der letzten Vorlesungsstunde: Radioaktive Zerfallsgeschwindigkeit, Altersbestimmungen, Ionisationszähler (Geiger-Müller-Zähler), Szintillationszähler, natürliche radioaktive Zerfallsreihen,
Wiederholung der letzten Vorlesungsstunde: Radioaktive Zerfallsgeschwindigkeit, Altersbestimmungen, Ionisationszähler (Geiger-Müller-Zähler), Szintillationszähler, natürliche radioaktive Zerfallsreihen,
Einblicke in die Mechanismen der Evolution durch Protein Design
 Der Biologie-Preis 2010 wurde Frau Birte Höcker, Tübingen,für ihre herausragenden Beiträge zum Verständnis der Evolution von Enzymen verliehen. Einblicke in die Mechanismen der Evolution durch Protein
Der Biologie-Preis 2010 wurde Frau Birte Höcker, Tübingen,für ihre herausragenden Beiträge zum Verständnis der Evolution von Enzymen verliehen. Einblicke in die Mechanismen der Evolution durch Protein
Die Sprache der Proteine Evolution konservierter Proteinstrukturen
 Die Sprache der Proteine Evolution konservierter Proteinstrukturen Andrei Lupas Max Planck Institut für Entwicklungsbiologie Tübingen Leben beruht auf der chemischen Aktivität von Proteinen Das Innere
Die Sprache der Proteine Evolution konservierter Proteinstrukturen Andrei Lupas Max Planck Institut für Entwicklungsbiologie Tübingen Leben beruht auf der chemischen Aktivität von Proteinen Das Innere
Molekularbiologie 6c Proteinbiosynthese. Bei der Proteinbiosynthese geht es darum, wie die Information der DNA konkret in ein Protein umgesetzt wird
 Molekularbiologie 6c Proteinbiosynthese Bei der Proteinbiosynthese geht es darum, wie die Information der DNA konkret in ein Protein umgesetzt wird 1 Übersicht: Vom Gen zum Protein 1. 2. 3. 2 Das Dogma
Molekularbiologie 6c Proteinbiosynthese Bei der Proteinbiosynthese geht es darum, wie die Information der DNA konkret in ein Protein umgesetzt wird 1 Übersicht: Vom Gen zum Protein 1. 2. 3. 2 Das Dogma
Vertiefendes Seminar zur Vorlesung Biochemie
 Vertiefendes Seminar zur Vorlesung Biochemie 07.11.2014 Proteine: Faltung Gerhild van Echten-Deckert Fon. +49-228-732703 Homepage: http://www.limes-institut-bonn.de/forschung/arbeitsgruppen/unit-3/abteilung-van-echten-deckert/abt-van-echten-deckert-startseite/
Vertiefendes Seminar zur Vorlesung Biochemie 07.11.2014 Proteine: Faltung Gerhild van Echten-Deckert Fon. +49-228-732703 Homepage: http://www.limes-institut-bonn.de/forschung/arbeitsgruppen/unit-3/abteilung-van-echten-deckert/abt-van-echten-deckert-startseite/
Kapitel 3 Ereignisdiskrete Systeme (III)
 Systemmodellierung Teil 1: Ereignisdiskrete Systeme Kapitel 3 Ereignisdiskrete Systeme (III) Modellierung mit E/A-Automaten Modellbildung mit Automaten Verfeinerte Modellbildung Beispiel: Fahrstuhltür
Systemmodellierung Teil 1: Ereignisdiskrete Systeme Kapitel 3 Ereignisdiskrete Systeme (III) Modellierung mit E/A-Automaten Modellbildung mit Automaten Verfeinerte Modellbildung Beispiel: Fahrstuhltür
Zurich Open Repository and Archive. Anatomie von Kommunikationsrollen. Methoden zur Identifizierung von Akteursrollen in gerichteten Netzwerken
 University of Zurich Zurich Open Repository and Archive Winterthurerstr. 190 CH-8057 Zurich http://www.zora.uzh.ch Year: 2008 Anatomie von Kommunikationsrollen. Methoden zur Identifizierung von Akteursrollen
University of Zurich Zurich Open Repository and Archive Winterthurerstr. 190 CH-8057 Zurich http://www.zora.uzh.ch Year: 2008 Anatomie von Kommunikationsrollen. Methoden zur Identifizierung von Akteursrollen
Wheeler s Delayed Choice - Einzelphotoneninterferenz. Judith Lehnert Dezember 2007 Seminar Moderne Optik
 Wheeler s Delayed Choice - Einzelphotoneninterferenz Judith Lehnert Dezember 2007 Seminar Moderne Optik Gliederung Theoretische Betrachtung: Gedankenexperiment Experimentelle Durchführung: Übersicht über
Wheeler s Delayed Choice - Einzelphotoneninterferenz Judith Lehnert Dezember 2007 Seminar Moderne Optik Gliederung Theoretische Betrachtung: Gedankenexperiment Experimentelle Durchführung: Übersicht über
Molekularbiologische Datenbanken
 Molekularbiologische Datenbanken Übungen Sommersemester 2004 Silke Trißl Prof. Ulf Leser Wissensmanagement in der Bioinformatik Organisatorisches Mittwoch 11 13 Uhr, RUD26 0'313 Mi, 05. Mai 2004 entfällt
Molekularbiologische Datenbanken Übungen Sommersemester 2004 Silke Trißl Prof. Ulf Leser Wissensmanagement in der Bioinformatik Organisatorisches Mittwoch 11 13 Uhr, RUD26 0'313 Mi, 05. Mai 2004 entfällt
VGM. VGM information. HAMBURG SÜD VGM WEB PORTAL - USER GUIDE June 2016
 Overview The Hamburg Süd VGM-Portal is an application which enables to submit VGM information directly to Hamburg Süd via our e-portal web page. You can choose to insert VGM information directly, or download
Overview The Hamburg Süd VGM-Portal is an application which enables to submit VGM information directly to Hamburg Süd via our e-portal web page. You can choose to insert VGM information directly, or download
Schulcurriculum für die Einführungsphase (11. Jahrgang)
 Schulcurriculum für die (11. Jahrgang) Material Unterrichtsinhalte Kompetenzen Unterrichtseinheit 1 Bau und Funktion von Biomembranen Zellbiologie Chemische Grundlagen: Kohlenhydrate - Proteine Lipide
Schulcurriculum für die (11. Jahrgang) Material Unterrichtsinhalte Kompetenzen Unterrichtseinheit 1 Bau und Funktion von Biomembranen Zellbiologie Chemische Grundlagen: Kohlenhydrate - Proteine Lipide
Wächtershäuser. Leben auf Erde an Oberfläche von Sulfiden entstanden
 Wächtershäuser Leben auf Erde an Oberfläche von Sulfiden entstanden Bildung von Biomolekülen an verlässliche Energieversorgung gekoppelt -> Energie durch Reduktion von Eisen in Eisen-Schwefel Mineralien
Wächtershäuser Leben auf Erde an Oberfläche von Sulfiden entstanden Bildung von Biomolekülen an verlässliche Energieversorgung gekoppelt -> Energie durch Reduktion von Eisen in Eisen-Schwefel Mineralien
