Biochemisches Praktikum 2
|
|
|
- Hinrich Seidel
- vor 10 Jahren
- Abrufe
Transkript
1 DEPARTMENT für BIOCHEMIE der LUDWIG-MAXIMILIANS-UNIVERSITÄT MÜNCHEN Biochemisches Praktikum 2 (Fortgeschrittenenpraktikum) Wintersemester 2014 Proteinfaltung Dr. Gregor Witte ([email protected]) Kurs 2: (Maksym, Schlauderer, Soberon) Kurs 1: (Butryn, Popova, Andreeva)
2 2. Kurswoche: Proteinfaltung Mo / Di / Mi / Do / Fr / Vorbesprechung: Denaturierungskurve EGFP, Fluoreszenz, Faltung Versuch: - Vorversuch In welchem Bereich denaturiert EGFP - Denaturierungsexperiment ansetzen und im Platereader messen - Auswertung der Kurve (Bradford Eichgerade) Einführung: Expression und Reinigung von nativer und denaturierter TEV- Protease Vorlesung: "Heterologe Expressionssysteme in E. coli" Vorbesprechung: Expression und Reinigung von nativer und denaturierter TEV- Protease Versuch : - Ansetzen von Puffern, Gießen von Gelen für SDS-PAGE - Zelllyse Stamm B Vorbesprechung: Expression und Reinigung von nativer und denaturierter TEV- Protease Versuch: - Zelllyse Stamm A - Reinigung von nativer TEV Protease - Präparation von inclusion bodies - Resolubilisierung der inclusion bodies und denaturierende Reinigung von TEV Protease - Rückfaltung durch Dialyse (über Nacht) Überblick über die Kurswoche, Arbeiten im Labor, Auswertung, Grundlage der Bewertung Vorbesprechung: Präparative Rückfaltung der denaturierten TEV Protease Versuch : - SDS-PAGE zur Dokumentation des Reinigungsverlaufs - TEV Protease Aktivitätstest - Präparation eines nativen Proteins via Fusions-Vorstufe - SDS-PAGE zum Aktivitätstest der TEV-Protease Vorbesprechung: Thermofluor Versuch: - Pipettieren der unterschiedlichen Pufferbedingungen Assay in der RealtimePCR Besprechung und Diskussion der Ergebnisse
3 Proteinfaltung 3 Einleitung Funktion, Struktur und Faltung Die Funktion eines Proteins wird durch seine Tertiärstruktur bestimmt, d.h. die Polypeptidkette muss sich nach der Translation in eine für dieses Protein charakteristische dreidimensionale Struktur falten. Nur die korrekt gefaltete "native" Struktur besitzt die für die biologische Aktivität eines Proteins wichtigen aktiven Zentren und Substratbindungsstellen. Die Proteinfaltung ist jedoch ein störanfälliger Prozess, da ungefaltete oder partiell gefaltete Proteine durch die Exposition hydrophober Bereiche leicht aggregieren oder sogar toxische Amyloid-Strukturen ausbilden können. In lebenden Zellen wird die Proteinfaltung deshalb von einer eigenen Klasse von Proteinen, den molekularen Chaperonen, unterstützt. Energielandschaften und Faltungstrichter Man kann mindestens zwei Zustände eines Proteins unterscheiden: den entfalteten Zustand (denatured state, D) und den nativen, gefalteten, funktionalen Zustand (native state, N). Bei idealer Reversibilität stehen die Zustände N und D im Gleichgewicht miteinander, d.h. Proteine entfalten sich spontan und falten wieder in den nativen Zustand zurück. Welcher Anteil einer Population eines Proteins gefaltet und entfaltet ist, ergibt sich aus dem Unterschied der Standard freien Energie der beiden Zustände ( G). In Analogie zur thermodynamischen Betrachtung von chemischen Reaktionen lässt sich Proteinfaltung in einem zweidimensionalen Energiediagramm mit den Energieniveaus von D und N und einem energiereichen Übergangszustand (transition state, T) dargestellen. Die Faltung von Polypeptidketten unterscheidet sich allerdings von chemischen Reaktionen dadurch, dass (i) D ein Ensemble einer großen Zahl von denaturierten Zuständen repräsentiert, und (ii) alternative, parallele Faltungswege existieren. In manchen neueren Modellen wird deshalb Proteinfaltung mit Hilfe von "Faltungstrichtern" und "Energielandschaften" veranschaulicht (Abb. 1). Sämtliche nicht-nativen Konformationen besitzen eine höhere Energie als die native Struktur, die den thermodynamisch günstigsten Zustand darstellt, und streben daher Konformationen niedrigerer Energie an. Ein Faltungstrichter repräsentiert dabei die vielen unterschiedlichen Faltungswege, die je nach Gestalt des Trichters schnell oder langsam zum energieärmsten Punkt (native Struktur) führen.
4 Proteinfaltung 4 Abb. 1 Der Faltungstrichter stellt die freie Energie (vertikale Achse) aller möglichen Proteinstrukturen als Funktion der konformationellen Freiheitsgrade dar (horizontale Achsen). Proteinfaltung in vivo Aufgrund der prinzipiellen Reversibilität der Proteinfaltung in vitro wurde zunächst angenommen, dass Proteinfaltungsprozesse auch in vivo spontan ablaufen. Dabei wurde ignoriert, dass in lebenden Zellen für Proteinfaltung höchst ungünstige Bedingungen herrschen. Dies trifft in erster Linie für die extrem hohen intrazellulären Proteinkonzentrationen von etwa mg/ml zu, aber auch für die Temperatur, die bei mesophilen Organismen meist zwischen 30 und 40 C liegt. Beide Bedingungen begünstigen stark die mit der Faltung zur nativen Konformation in Konkurrenz stehende Aggregation von Faltungsintermediaten. In vitro dagegen wird ein erfolgreicher Verlauf von Proteinfaltungsreaktionen in der Regel nur bei starker Verdünnung und niedrigeren Temperaturen beobachtet. Des weiteren besitzen zelluläre Proteine Molekulargewichte von bis zu vielen hundert kda bei einem durchschnittlichen Molekulargewicht von etwa kda, und sind damit deutlich größer als viele der bei in vitro Rückfaltungsexperimenten typischerweise eingesetzten Modellproteine. Mit steigender Polypeptidlänge nimmt aber die Anzahl alternativer, d. h. nicht-nativer, Konformationen exponentiell zu. Dieser kurze Vergleich macht deutlich, dass die Faltung eines in vivo neusynthetisierten Proteines in die native Konformation nicht alleine aufgrund der aus zahlreichen in vitro-studien gewonnenen Erkenntnisse verstanden werden kann. Tatsächlich existieren zwei wesentliche Unterschiede zwischen der Proteinfaltung in vivo und in vitro. Zum einen ist die Translation ein vektorieller Vorgang, der die geordnete, kotranslationale Ausbildung der Sekundär- und Tertiärstruktur einzelner Domänen ermöglicht. Dadurch ist die Anzahl alternativer Faltungsintermediate drastisch reduziert und gleichzeitig nahezu unabhängig von der Gesamtlänge des Proteins. Zum zweiten besitzen alle Zellen eine Klasse von Proteinen, die sogenannten "molekularen Chaperone", welche die produktive Faltung neusynthetisierter, translozierter oder denaturierter Proteine unterstützen. Molekulare Chaperone Molekulare Chaperone wirken durch relativ unspezifische stöchiometrische Interaktionen mit faltenden, oligomerisierenden, inaktiven und denaturierten Proteinen, ohne Teil von deren nativer Struktur zu sein. Chaperone sind nicht nur bei der Faltung de novo synthetisierter Proteine involviert, sondern besitzen
5 Proteinfaltung 5 darüberhinaus essentielle Funktionen bei der Aggregationsverhinderung und der Rückfaltung denaturierter Proteine, z. B. nach Temparaturstress. Die meisten Chaperone wurden daher ursprünglich als sogenannte "Hitzeschockproteine" (Hsp s) beschrieben und nach ihrem ungefähren Molekulargewicht in die Familien Hsp100, Hsp90, Hsp70, Hsp60 und Hsp27/28 eingeteilt. Diese evolutionär hochkonservierten Familien besitzen untereinander keine signifikante Homologie und durchaus unterschiedliche spezifische Funktionen. Allen Chaperonen gemeinsam ist jedoch die sie definierende Fähigkeit, die Aggregation wenigstens einzelner denaturierter Proteine zu verhindern und dadurch deren Rückfaltungsausbeute zu erhöhen. Am besten verstanden ist die Funktion der Hsp60 Familie, insbesondere des Vertreters aus E. coli, GroEL. GroEL ist ein symmetrischer, aus zwei heptameren Ringen bestehender tetradekamerer Komplex mit einem Molekulargewicht von 812 kda. Zusammen mit dem heptameren Kofaktor GroES (84 kda) und unter ATP- Verbrauch unterstützt GroEL die korrekte Faltung einer Vielzahl von de novo synthetisierten und denaturierten Proteinen in E. coli. Die Raumstruktur des GroELS Komplexes ist bekannt (Abb. 2). Der GroEL Doppelring umschließt zwei mit hydrophoben Bindungsstellen ausgekleidete Höhlen, in denen Substratproteine gebunden werden. Die in der Regel asymmetrisch an nur einem Ring erfolgende Anlagerung eines GroES Heptamers führt zu einer dramatischen Konformationsänderung dieses Ringes, bei der die substratbindende Höhle deutlich vergrößert und gleichzeitig eine hydrophilere Oberfläche präsentiert wird. Zahlreiche biochemische Untersuchungen mit Modellsubstraten und unterschiedlichen GroEL- Mutanten haben ein sehr detailliertes Bild des Mechanismus der GroELS Chaperonfunktion ergeben (Abb. 3). Denaturierte oder aggregationsgefährdete Substratproteine werden durch die hydrophoben Bindestellen des GroES- und nukleotidfreien GroEL-Ringes gebunden. 7 Moleküle ATP werden mit positiver Kooperativität von diesem Ring gebunden, während der gegenüberliegende Ring gleichzeitig aufgrund negativer Kooperativität nukleotidfrei bleibt. Bindung von GroES an den Substrat- und ATP-bindenden Ring führt zur Vergrößerung der substratbindenden Höhle und macht deren Oberfläche hydrophiler. Gleichzeitig wird die Hydrolyse des gebundenen ATP stimuliert. Aufgrund der niedrigen ATPase- Aktivität von GroEL dauert die Hydrolyse aller 7 ATP-Moleküle etwa 15 Sekunden. In diesem Zeitraum, in dem das Substratprotein als einzelnes Molekül gewissermaßen unendlich verdünnt vorliegt und nicht mehr über hydrophobe Wechselwirkungen mit anderen Faltungsintermediaten oder der GroEL-Höhle wechselwirkt, kann es unter "optimalen" Bedingungen seine Faltung fortsetzen. Nach erfolgter ATP-Hydrolyse kann ATP am gegenüberliegenden Ring binden, was zur Dissoziation von GroES, Substrat und ADP führt. Das Substrat befindet sich nun entweder im nativen oder einem faltungskompetenten Zustand, oder aber es ist nach wie vor aggregationsgefährdet und nicht faltungskompetent. In diesem Fall wird es erneut gebunden und durchläuft einen weitern Zyklus der GroELS Chaperonaktivität.
6 Proteinfaltung 6 Abb. 2 Kristallstruktur (a) einer GroEL Untereinheit; (b) des GroEL-Komplexes; (c) des GroEL- ADP-GroES-Komplexes Abb. 3 Funktioneller Zyklus des GroELS Chaperonsystems. GroELS sind schematisch als Längsschnitt dargestellt Heterologe Expression von Proteinen in E. coli Eine wichtige Grundlage in der modernen Biochemie ist die Expression von Fremdproteinen vor allem in E. coli. Diese heterologe Expression ermöglicht es beispielsweise, humane Proteine in ausreichenden Mengen für biochemische Untersuchungen oder Strukturanalysen herzustellen. Allerdings lassen sich nicht alle eukaryontischen Proteine problemlos in E. coli herstellen. Das kann verschiedene Ursachen haben. Zum einen kann aufgrund der unterschiedlichen Codon-Häufigkeit in Pro- und Eukaryoten oder von mrna-sekundärstrukturbildungen die Translationseffizienz sehr gering sein, d.h. die Proteine werden nur in geringen Mengen oder überhaupt nicht synthetisiert. Andere Proteine werden zwar effizient synthetisiert, falten aber nicht in ihre native Konformation, entweder weil diese Disulfidbrücken aufweist, die sich im reduzierenden E. coli Cytosol nicht ausbilden, oder weil aufgrund der Überexpression zu wenig Chaperone vorhanden sind, um die vorzeitige Aggregation zu verhindern. Häufig führt deswegen die heterologe Überexpression in E. coli zur Ablagerung des unlöslichen, aggregierten Proteins in sogenannten "inclusion bodies" (= Einschlußkörpern). Um dennoch natives Protein zu erhalten, können zwei unterschiedliche Strategien verfolgt werden. Entweder werden die Expressionsbedingungen durch Variieren von Temperatur, Expressionsstärke, Medium sowie durch den Einsatz von Fusionskonstrukten (s. u.) so optimiert, dass lösliches Produkt hergestellt wird. Alternativ kann das Protein durch Denaturierungsmittel aus inclusion bodies gelöst, im denaturierten Zustand gereinigt, und dann in vitro renaturiert werden.
7 Proteinfaltung 7 Fusionsproteine Bei schwer zu synthetisierenden oder schwer zu isolierenden Proteinen kann durch die Verwendung von sogenannten Fusionsproteinen die Expression und / oder die Reinigungseffizienz oft deutlich verbessert werden. Dazu wird ein Fusionskonstrukt hergestellt, bestehend aus einem Hilfsprotein oder -peptid, an das über einen kurzen Linker das Zielprotein fusioniert ist (Abb. 5). Das Hilfsprotein wird in E. coli hocheffizient synthetisiert und gefaltet. Als Fusion mit dem Zielprotein hilft es, dieses zu synthetisieren, seine Faltung zu ermöglichen, und das gefaltete Zielprotein löslich zu halten. Abb. 5 Schematische Darstellung eines Fusionsproteins Oft lässt sich das Hilfsprotein oder peptid auch zur Reinigung des Fusionsproteins nutzen. Z. B. lassen sich Maltose Bindendes Protein (MBP) enthaltende Fusionsproteine sehr effizient durch Amylose-Affinitätschromatographie reinigen. Die Fusion mit einem Hexahistidin-tag, ermöglicht die Reinigung des Fusionsproteins durch immobilisierte Metallionen-Affinitätschromatographie (IMAC). Die Aminosäure Histidin bildet Komplexe mit zweiwertigen Metallionen, z. B. Ni 2+ (Abb. 6). Durch Hexahistidin-tags wird die Affinität des Fusionsproteins zu Ni 2+ -Ionen verstärkt (lokal hohe Chelator-Konzentration). An eine Matrix gekoppelte Nitrilo-tri-Essigsäure (NTA) komplexiert Ni 2+ auf einer Chromatographie-Säule, so dass Fusionsproteine nach Bindung oft in einem Schritt zur Homogenität gereinigt werden können. Die Elution erfolgt durch Kompetition mit Imidazol, welches die Histidinreste verdrängt (Ligandenaustausch am Ni 2+ ); durch Absenken des ph-wertes auf 4.5 (Protonierung der Histidinreste); oder durch EDTA (Chelation und Ablösung der Ni 2+ -Ionen von der NTA-Matrix).
8 Proteinfaltung 8 Abb. 6 Ein matrixgekoppelter Ni 2+ -NTA-Chelatkomplex koordiniert die Imidazolfunktionen zweier Histidinseitenketten. Für viele biochemische Untersuchungen kann das Fusionsprotein direkt verwendet werden, da das aktive Zentrum des Zielproteins meist zugänglich ist. Oft ist es jedoch notwendig, das Hilfsprotein nach der Expression und Reinigung abzuspalten, um natives Zielprotein zu erhalten. Die Spaltung erfolgt durch limitierte Proteolyse mit einer spezifischen Protease, deren Erkennungssequenz der Linker des Fusionsproteins enthält. Eine der für diesen Zweck am besten geeigneten Proteasen ist die Protease aus Tobacco Etch Virus (TEV). Die ~27 kda große TEV Protease erkennt die Heptapeptid-Sequenz E-X-X-Y-X-Q S/G. Die Proteolyse erfolgt zwischen Q und S/G. Im Gegensatz zu vielen anderen Proteasen wie etwa Trypsin, Thrombin oder Faktor Xa, ist die TEV Protease äußerst spezifisch, so dass das Zielprotein in der Regel intakt bleibt. Ein weiterer Vorteil der TEV Protease gegenüber anderen Proteasen ist die relativ robuste Aktivität unter verschiedenen Pufferbedingungen (ph, Salzkonzentration u.ä.). Somit können für die Proteolyse Bedingungen gewählt werden, die für die Stabilität des Zielproteins optimal sind. In vitro Renaturierung Die Ablagerung eines überexprimierten Proteines (Abb. 7) kann durchaus von Vorteil sein. In inclusion bodies wird meistens nur das aggregierte Fremdprotein abgelegt, welches deshalb bereits relativ rein und in sehr hoher Konzentration vorliegt. Es lässt sich in Form der inclusion bodies leicht aus den Zellen gewinnen. Zudem ist das Protein vor dem Abbau durch zelluläre Proteasen geschützt. Die in inclusion bodies aggregierten unlöslichen Proteine können allerdings nur mit stark denaturierenden Agenzien wieder in Lösung gebracht werden. Meist werden hierfür Puffer mit hohen Konzentrationen von Harnstoff oder Guanidiniumchlorid verwendet. Die genaue Wirkung dieser Substanzen ist unbekannt. Guanidiniumchlorid als ein chaotropes Salz scheint die Wasserstoffbrücken in
9 Proteinfaltung 9 Proteinen, aber auch im Lösungsmittel zu stören. Eine Interpretation ist, dass Guanidiniumchlorid die Unordnung in flüssigem Wasser erhöht. Dadurch werden die hydrophoben Seitenketten im Kern des Proteins leichter löslich und das Protein wird denaturiert. Gleiches gilt für die intermolekularen hydrophoben Wechselwirkungen in Proteinaggregaten. Diese Eigenschaft macht man sich zunutze, um Proteine aus inclusion bodies zu lösen, zu reinigen und sie anschließend in ihre native Struktur zu überführen (= Renaturierung). Dazu müssen die denaturierenden Agenzien wieder entfernt werden. Das Problem dabei ist, die Konzentration des Denaturierungsmittels zu vermindern, um die Faltung zu erlauben, dabei aber die Aggregation der Proteine zu verhindern. Häufig wird zum Entfernen des Denaturierungsmittels die Dialyse angewendet. Diese Methode ist einfach, schnell und leicht durchführbar. Dabei wird das im Denaturierungsmittel gelöste Protein gegen ein großes Volumen eines Puffers ohne Denaturierungsmittel dialysiert. Während der Dialyse verringert sich die Konzentration des Denaturierungsmittels relativ langsam. Bei mittleren Konzentrationen des Guanidiniumchlorids beginnt sich das Protein wieder zu falten, während die Aggregation oft noch verhindert wird. Das Faltungsgleichgewicht wird also langsam vom denaturierten Zustand zum naturierten Zustand verschoben. Abb. 7 Elektronenmikroskopische Aufnahme von Bakterienzellen mit inclusion bodies. Das in Bakterienzellen überproduzierte Fremdprotein kann sich nicht korrekt falten und bildet sehr große, unlösliche Aggregate (inclusion bodies).
10 Proteinfaltung 10 Versuch 1: Entfaltung von egfp, Denaturierungskurve Die biologisch aktive Form eines Proteins (native Faltung) wrid im allgemeinen durch eine Kombination aus nicht-kovalenten Wecheselwirkungen erreicht. Das nativ gefaltete Protein ist dabei normalerweise im energetischen Minimum des Faltungstrichters. Die freie Enthalpie des gefalteten Zustands ist also in der nativen Umgebung des Proteins negativ. Im Umkehrschluß bedeutet das, dass evtl. homologe Proteine aus unterschiedlichen Spezies, die in anderen Umgebungen leben auch unterschiedlich stabil sind, weil die Faltung (und das G) eine Funktion der Temepratur, Salzgehalt, ph etc. ist. Beispielsweise muss eine DNA-Polymerase zwar in den folgenden Spezies immer die gleiche aufgabe erfüllen - aber das Enzym muss für jede Spezies eine andere stabilität aufweisen: Spezies optimales Wachstum Homo sapiens 37 C Thermus aquaticus >75 C Sulfolobus solfataricus C, ph 2-3 (!) Halobacterium salinarium 2.5 M - 5M NaCl (!) Pyrococcus furiosus 100 C Offensichtlich wird eine humane DNA polymerase unter den Wachstumsbedingungen von P.furiosus nicht mehr im nativen Zustand vorliegen und umgekehrt ein Protein aus dem halophilen H.salinarium in Bedingungen mit wenig Salz nicht nativ gefaltet sein. Durch den Evolutionsdruck wurden in extremophilen Organismen bestimmte Eigenschaften selektiert, z.b. der GC-gehalt der DNA (höherer Schmelzpunkt) und auf Proteinebene eine höhere Stablität der Proteine (mehr geladene Aminosäuren, mehr Salzbrücken). Um Aussagen über die Stabilität eines Proteins zu treffen werde normalerweise Denaturierungs/Renaturierungsexperimente durchgeführt, bei der die Faltung des Proteins in Gegenwart von Entfaltungsfaktoren beobachtet wird. Diese Faktoren können zum Beispiel Temperatur, ph oder denaturierende Chemikalien sein. Die Faltung des Proteins selbst kann auf verschiedene Weise "gemessen" werden, hier nur einige Beispiele: Circulardichroismus (misst Strukturanteile) Änderungen im hydrodynamischen Radius (z.b. in dynamischer Lichtstreuung) Änderung intrinsischer Faktroren, z.b. Fluorezenz Änderung von Signalen einer "Entfaltungssonde", z.b. im Thermofluor- Experiment: Zugabe eines Farbstoffs, der eine andere Fluoreszenz zeigt wenn er an entfaltetes Protein bindet
11 Proteinfaltung 11 Änderung der Funktion/Aktivität eines Proteins Ein typisches Experiment wäre zum Beipiel das Schmelzen eines Proteins unter gleichzeitiger Messung der Strukturparamter mit CD. Während der Entfaltung werden die strukturierten Anteile (beta sheets, alpha helices) kollabieren und die entsprechenden Signale im CD Änderung zeigen. Eine weitere übliche Methode ist die Entfaltung mit dem chaotropen Agens Guanidiniumhydrochlorid. GuaHCl ist ein chaotropes Salz, dass einen recht starken Einsalzeffekt hat (Hofmeister Reihe): Präzipitation Solubilisieren Im Prinzip ähnelt ein Entfaltungsexperiment einer Titration - die Änderung der Faltung wird als Funktion des denaturierenden Faktors gemessen - also z.b. %Faltung vs. [GuaHCl] (Entfaltungskurve). Um die Stabilität eines Proteins quantitativ beschreiben zu können, kann man diese Denaturerungskurven thermodynamisch auswerten. Voraussetzung dafür ist, dass die Entfaltung reversibel ist - also ein Gleichgewicht vorliegt. Im einfachsten Fall gibt es bei der Entfaltung zur zwei Zustände, also natives Protein (N) und entfaltetes Protein (U) und keine Intermediate. Man spricht dabei von einem alles-oder-nichts Modell. Natives Protein (N) entfaltetes Protein (U) (1) Die Gleichgewichtskonstante K d der Denaturierung ist dann gegeben durch: K d = [U] / [N] (2) und die Änderung der freien Enthalpie bei der Entfaltung nach Gibbs: G d = - R T ln K d (3) G d kann experimetell in zwei Schritten bestimmt werden: Aliquots des zu denaturierenden Proteins werden mit unterschiedlichen Mengen GuaHCl versetzt und inkubiert bis sich das Gleichgewicht eingestellt hat.
12 Proteinfaltung 12 Um Kd zu bestimmen benötigt man eine Eigenschaft die proportional zum Anteil des gefalteten Proteins (oder des ungefalteten) ist. Im Experiment wird egfp (enhanced GFP; 39,2 kda, 346 aa) als Protein verwendet, dass bei Anregung (Excitation) mit 488nm eine charakteristische grüne Fluoreszenz (Emission) bei 516nm zeigt. Abbildung 8: Absorptionsspektrum und Emissionsspektrum von enhanced GFP. Bei einem fluoreszierenden Protein wie GFP kann man in erster Näherung davon ausgehen dass nur das native Protein fluoresziert und das entfaltete Protein garnicht (würden sie sagen dass das richtig ist?). Im Assay entspricht also die gemessene Fluoreszenz einer Art Anteil an nativem GFP (f native ). Die Denaturierungskurve (normalerweise Fluoreszenzintesität vs. [GuaHCl] ) lässt sich somit durch einfache normierung in eine Kurve %natives Protein (f native ) vs. [GuaHCl] umwandeln (also f n (0M GuaHCl)=1 und f n (total entfaltet)= 0, f u = 1- f n ) ). Voraussetzung ist natürlich das man f n =1 und f n =0 auch in der Kurve eindeutig bestimmen kann - also nicht nur der Übergangsbereich vorhanden ist.
13 Proteinfaltung 13 Abbildung 9: Beispiel für eine normierte Entfaltungskurve. Mit den so bestimmten Anteilen f n und f u können für jeden Punkt der Denatutrierungskurve die Gleichgewichtskonzentrationen des gefalteten und ungefalteten Proteins mit Hilfe der bekannten Ausgangskonzentrationen berechnet werden. Offensichtlich ist fn vor dem Übergangsbereich immer ~1 und nach dem Entfaltungsbereich ~0. Der für die Kd-Bestimmung wichtige Bereich ist also der Bereich des Übergangs fn fu. Berechnet wird für jede GuaHCl-Konzentration im Übergangsbeirechi ein K d (2) und ein G (3). Die so erhaltenen Werte von G [GuaHCl] verhalten sich in erster Näherung linear zu den Konzentrationen GuaHCl: G [GuaHCl] = G (H2O) m [GuaHCl] (4) Damit kann die freie Enthalpie der Entfaltung in Abwesenheit von GuaHCl durch extrapolation bestimmt werden. Alle in diesem Praktikumsteil durchgeführten Messungen werden mit einem 96well- Platten Platereader (Tecan F200pro) mit Proben in einer 96well-Platte durchgeführt (bitte merken was wo pipettiert wurde!). Bitte die Platte an der Seite beschriften (Gruppe od. Namen, Datum).
14 Proteinfaltung 14 Das Volumen pro Reaktionsansatz beträgt 200µl. Sie benötigen folgende Puffer: bitte im 15ml Falcontube herstellen (Stocklösungen verwenden) 6M GuaHCl-Puffer (15ml) 6M Guanidiniumhydrochlorid 200mM NaCl 20mM Tris ph7.2 egfp-puffer (15ml) 200mM NaCl 20mM Tris ph7.2 Vorexperiment Wie bereits festgestellt, ist der wirklich interessante Bereich der Denaturierungskurve der Übergangsbereich. Um möglichst viele Messpunkte in diesem Bereich zu haben wird in eine Vorversuch gemessen, wo der Übergangsbereich in etwa liegt. Dazu werden relativ grobe Abstände in der GuaHCl-Konzentration gewählt. Bitte berechnen Sie die benötigten Mengen Puffer für einen Reaktionsansatz von 200µl. GuaHCl (M) egfp Puffer (µl) 6M GuaHCl Puffer (µl) Protein (µl)
15 Proteinfaltung 15 Die Ansätze werden direkt in die 96well Platte pipettiert (z.b. Reihe A) und zwar in der angegebenen Reihenfolge: 1. erst egfp-puffer, 2. dann 6M GuaHCl-Puffer 3.und zuletzt das Protein. Danach wird vorsichtig durch auf- und abpipettieren von 50µl gemischt. Bitte Luftblasen vermeiden - falls doch welche entstehen: mit einer kleinen Pipettenspitze versuchen sie zu entfernen (Crystaltips). Luftblasen stören die Fluoreszenzmessungen! Nach dem Mischen werden die Platten mit Tesafilm/CrystalClear-Tape versiegelt. 1. Inkubation 15min Raumtemperatur 2. Messen der Fluoreszenz im Tecan F200pro (dazu das Tape abziehen?) 3. Inkubation der zugeklebten Platte für 15-30min bei 37 C im Brutschrank 4. Messen der Fluoreszenz im Platereader (bei 37 C) Bitte tragen sie die gemessenen Fluoreszenzwerte gegen die Konzentration an Guanidiniumhydrochlorid auf (für beide Temperaturen). Kann man die Raumtemperaturkurve auswerten? Denaturierungskurve mit Übergangsbereich Der im Vorexperiment bestimmte Konzentrationsbereich des Übergangs wird mit mehr Messpunkten erneut untersucht. Es werden einfach zu pipettierende Volumina bei den Ansätzen verwendet (z.b. 5µl Schritte) - die Konzentrationen an GuaHCl für die Denaturierungskurve können anhand der pipettierten Volumina einfach ausgerechnet werden. Für den Übergangsbereich ± 1M GuaHCl bitte kleine Abstände (5µl) verwenden, bei den anderen Punkten reichen 10µl Abstände. Sie brauchen auch die Werte in den Plateaus nocheinmal (mit weniger Punkten). Eine solche GuaHCl-Reihe könnte z.b. so aussehen (in M) : 0, 1, 1.5, 2.5, 3.0, 3.15, 3.3, 3.45, 3.6, 3.75, 4.0 (..) Verfahren sie wie vorher: 1. Piepttieren in die 96well Platte (egfp-puffer, GuaHCl-Puffer, Protein + mischen 2. Versiegeln der Platte 3. Inkubation bei 37 C 15-30min 4. Messen der Fluoreszenz 5. Inkubation über Nacht und nochmaliges messen am folgenden Tag.
16 Proteinfaltung 16 Auswertung: 1. Vorexperiment Plot: Fluoreszenzintensität vs. [GuaHCl] Welcher Bereich ist interessant? 2. Denaturierungskurve - Plot Fluoreszenzintensität vs. [GuaHCl] - normierter Plot %gefaltet vs. [GuaHCl] [GuaHCl] - Für den Übergangsbereich tabellarisch K d und G [GuaHCl] - Plot: G [GuaHCl] vs. [GuaHCl], extrapolation von G (mathematisch) auf [GuaHCl]=0M, Gleichung angeben. - berechnen G pro Rest des Proteins. Beantworten Sie im Protokoll bitte auch folgende Fragen: - Ist egfp ein typisches Protein oder besonders stabil/instabil? - Ist das System nach 15min schon im Gleichgewicht? Vergleich mit den Übernacht-Inkubationen - Ist die Annahme gerechtfertigt dass es sich um einen Alles-oder-nichts- Übergang handelt?
17 Proteinfaltung 17 Versuch 2: Expression, Reinigung und Renaturierung von rekombinanter Tobacco Etch Virus (TEV) Protease Als Beispiel für heterologe Proteinexpression in E. coli wird im Praktikum rekombinante TEV Protease exprimiert und sowohl in nativer Form aus dem löslichen Zellextrakt als auch unter denaturierenden Bedingungen aus inclusion bodies gereinigt. Die denaturierend aufgereinigte Protease wird durch Dialyse renaturiert, und die nativen und renaturierten Enzympräparationen werden im Hinblick auf Ausbeute, Reinheit und proteolytische Aktivität gegen ein Fusionsprotein miteinander verglichen. Für die Expression der TEV Protease wird das T7 System verwendet. Im verwendeten Expressionsplasmid steht das Gen für die TEV Protease unter der Kontrolle des sehr starken Promotors des Bacteriophagen T7. Dieser Promoter wird nicht von der E. coli RNA-Polymerase, sondern sehr spezifisch von der T7 RNA- Polymerase erkannt, d.h. es findet nur in Gegenwart der T7 RNA-Polymerase Transkription statt. Das Gen für die T7 Polymerase ist bei den speziell für das T7 System konstruierten E. coli Stämmen als λ Lysogen in das E. coli Chromosom integriert und steht unter der Kontrolle des lac Promotors mit dem lac Operator. Dies erlaubt die induzierte Expression der T7 Polymerase durch das nicht metabolisierbare Lactose-Analog Isopropyl-ß-D-thiogalactopyranoside (IPTG). Die so produzierte T7 RNA-Polymerase transkribiert dann sehr effizient vom T7 Promoter aus das Gen für die TEV Protease. Die TEV Protease wird von dem Expressionsplasmid als Hexahistidin-Fusionsprotein exprimiert, so dass sie unter nativen und denaturierenden Bedingungen durch Nickel- Affinitätschromatographie in einem Schritt gereinigt werden kann. Tag 1: Dienstag Geräte und Material: eppendorf Zentrifuge 5810R mit Rotor sowie passenden Röhrchen Fluidizer/Sonicator (?) Zubehör für SDS-Gelelektrophorese 5 ml-polypropylen-leersäulen mit Stativständer o.ä. Elektrophorese-Apparturen, Glasplatten, Spacer und Kämme für Minigele (BioRad) Falconröhrchen (15 und 50 ml) Spectrapor Dialyseschlauch mit Klemmen Molekulargewichtsstandard für SDS-PAGE pro Gruppe je ein gefrorenes Zellpellet (ca. 2.6 g Nassgewicht) von induzierten Expressionskulturen Stamm "A" und "B" Puffer und Lösungen (werden gestellt): Ni-NTA Agarose beads (Qiagen) BioRad Protein Assay Konzentrat 30% Acrylamid-Lösung (giftig!) TEMED gereinigtes His-Tag-Fusionsprotein, ca. 1 mg/ml
18 Proteinfaltung 18 Selbst anzusetzende Puffer und Lösungen (Angaben pro Gruppe, für alle Gruppen +1x Reserve entsprechendes Volumen erstellen und aliquotieren) ACHTUNG: Puffer A10 und F als erstes vorbereiten und sofort auf Eis stellen!!! ACHTUNG: Puffer zum Gießen der SDS-Gele als nächstes bereitstellen!!! ACHTUNG: Die angegebenen Puffer-Aliquotes sind reichlich berechnet, werden jedoch z.t. auch für Versuche 2 und 3 benötigt. Bitte nicht vorzeitig entsorgen!!! Sie fertigen die Ihnen zugeteilten Puffer für alle Gruppen an. Puffer A10: (150ml) 50 mm Natriumdihydrogenphosphat 10 mm Tris/HCl 150 mm NaCl 10 mm Imidazol mit NaOH oder HCl auf ph 8.0 einstellen Puffer A20: (50ml) 50 mm Natriumdihydrogenphosphat 500 mm NaCl 20 mm Imidazol mit NaOH oder HCl auf ph 8.0 einstellen Puffer A250: (50ml) 50 mm Natriumdihydrogenphosphat 500 mm NaCl 250 mm Imidazol mit NaOH oder HCl auf ph 8.0 einstellen Puffer B: (50ml) 6M Guanidinhydrochlorid 100mM Natriumdihydrogenphosphat 10mM Tris/HCl mit NaOH oder HCl auf ph 8.0 einstellen Puffer C: (50ml) 6M Harnstoff 100mM Natriumdihydrogenphosphat 10mM Tris/HCl mit NaOH oder HCl auf ph 8.0 einstellen Puffer D: (20ml) 6M Harnstoff 100mM Natriumdihydrogenphosphat 10mM Tris/HCl mit NaOH oder HCl auf ph 6.3 einstellen
19 Proteinfaltung 19 Puffer E: (5ml) 6M Harnstoff 100mM Natriumdihydrogenphosphat 10mM Tris/HCl mit NaOH oder HCl auf ph 4.5 einstellen Puffer F: (600ml) 500mM NaCl 100mM Tris/HCl 10% Glycerol 5mM DTT 0.5mM EDTA mit HCl auf ph 8.0 einstellen Stocklösungen für Puffer G, G2, H: 1. 1 M Tris/HCl, ph 7.6 (10 ml) 2. 5 M NaCl (10ml) 5x Puffer G: (10 ml) 500 mm Tris/HCl, ph M NaCl 5 mm EDTA 10 mm β-mercaptoethanol (β ME) 5x Puffer G2: (50 µl) 500 mm Tris/HCl, ph M NaCl 10 mm β-mercaptoethanol (β ME) 5x Puffer H: (10 ml) 50 mm Tris/HCl, ph M NaCl
20 Proteinfaltung 20 Puffer für SDS-PAGE Bitte nach Bedarf ansetzen, es werden auch Lösungen gestellt nur Herstellen, wenn es so aussieht als ob die Puffer knapp werden. 5x SDS-Gel Proben-Puffer (10 ml für kompletten Kurs, wird gestellt): 50% Glycerin 7.5% SDS 250 mm Tris/HCl ph 6.8 vor Zugabe von Bromphenolblau und DTT einstellen! (ca.!) 0.1% Bromphenolblau 100 mm Dithiothreitol (DTT) fertigen Puffer bei 4 C lagern; vor Gebrauch immer kurz (30 sec) aufkochen. 10 x SDS-PAGE Elektrophorese-Puffer (wird gestellt): Endkonz. Für 2 Liter (Kurswoche) 250 mm TRIS Base 60,57 g 1.92 M Glycin g 1% SDS 10%ige SDS Lösung 200 ml H 2 O Ad 2000 ml 1 L H 2 O vorlegen, Feststoffe unter Rühren lösen, dann SDS und Restwasser zugeben > bei diesem Puffer wird der ph nicht nachträglich eingestellt > er ergibt sich automatisch aus der Mischung von TRIS und Glycin!!!!! ph 8.3 Coomassie-Färber (wird gestellt): Endkonz. 1 Liter (reicht sicher für ein Labor) 50% EtOH (technisch) 500 ml 10% Essigsäure 100 ml 0.25% Coomassie Brillant Blue R g H 2 O 400 ml Coomassie Pulver in EtOH lösen + H 2 O > erst dann Eisessig zugeben > unter dem Abzug Coomassie Entfärber (wird gestellt): Endkonz. Für 2 Liter (pro Labor/Kurs) H 2 O 1000 ml 40% EtOH (technisch) 800 ml 10% Essigsäure 200 ml > unter dem Abzug
21 Proteinfaltung 21 Gießen von Polyacrylamid-Gelen für SDS-PAGE nach Lämmli (siehe auch Kurswoche Beatrix/Beckmann): Gießen von Polyacrylamid-Gelen für SDS-PAGE nach Lämmli: Handschuhe tragen Arbeitsplatz mit laminiertem Filterpapier (ca. DinA4 Blattgröße) vorbereiten. Glasplatten gründlich putzen (EtOH) und nach Anweisung der Assistenten in BioRad MiniProtean Gießständer einspannen. Vorsicht, Glasplatten brechen leicht! Überprüfen Sie die Dichtheit des Aufbaus mit H2O. Jeweils die folgenden Lösungen unter dem Abzug mischen (nicht mit Rainin Pipetten in die Acrylamid-Vorratsflasche gehen!!!). Benutzen Sie hier eine serologische 10 ml Einmalpipette mit ihrem Pipettboy oder Pilleus Ball. Jeweils die folgenden Lösungen Mischen Achtung: Insgesamt werden 2 Gele (1x 12 % Acrylamid, 15 Taschen; 1x 15 % Acrylamid, 15 Taschen) benötigt, die in zwei Durchgängen (15 % / 12 %) vorbereitet und gegossen werden. Stocklösungen (eizusetzende Mengen je nach Bedarf): M Tris/HCl, ph 8.8 (x ml) 2. 1 M Tris/HCl, ph 6.8 (x ml) 3. 10% SDS (x ml) 4. 10% Ammoniumpersulfat (APS; x ml; bei 4 C aufbewahren) 12% Trenngel (7,5 ml für 1 Gel): 2.5 ml H 2 O 3.0 ml 30% Acrylamid Stammlösung 2,0 ml 1.5 M Tris/HCl ph µl 10% SDS 4 µl TEMED Polymerisation starten durch Zugabe von APS! 75 µl 10% APS 15% Trenngel (7,5 ml für 1 Gel): 1.75 ml H 2 O 3.75 ml 30% Acrylamid Stammlösung 2.0 ml 1.5 M Tris/HCl ph µl 10% SDS 4 µl TEMED Polymerisation starten durch Zugabe von APS! 75 µl 10% APS Polymerisation starten durch Zugabe von 150 µl 10% APS für 2 Gele, mischen, blasenfrei in vorbereiteten Gelaufbau gießen, bis ca. 1.5 cm unterhalb der kürzeren Glaskante. Eine Markierung mit dem feinen Edding Filzschreiber ist hier hilfreich.
22 Proteinfaltung 22 Vorsichtig mit ca. 0.5 ml Isopropanol überschichten. Nach vollständiger Polymerisation Isopropanol abgießen und mit Filterpapier restlos entfernen. 5% Sammelgel (4.5 ml, für 2 Gele): 2.7 ml H2O 750 µl 30% Acrylamid 565 µl 1 M Tris/HCl ph µl 10% SDS 5 µl TEMED (pro 2 Gele) Polymerisation starten durch Zugabe von APS! 45 µl 10% APS Nach mischen, Lösung blasenfrei auf Trenngel pipettieren, Teflon-Kamm (10/15 Taschen) blasenfrei einschieben. Für das Gießen eines Gels entsprechend skalieren. Auspolymerisierte Gele werden in feuchte Zewa-Tücher und dann in Frischhaltefolie eingewickelt und sind im Kühlschrank einige Tage haltbar. Lyse der TEV Protease exprimierenden E. coli Zellen Am Dienstag nur die Zellpellets B aufschließen und das Rohe-IB-Pellet im Kühlschrank über Nacht aufbewahren. Das Zellpellet A wird am Mittwochmorgen aufgeschlossen. Zellpellet A = lösliche Expression; Zellpellet B = inclusion bodies - Der Zellaufschlüsse finden durch den Betreuer statt. (Die Zellpellets werden auf Eis aufgetaut, in 10 ml kaltem Puffer A10 vollständig resuspendiert und im Fluidizer oder Ultraschall aufgeschlossen (2 Läufe mit Zellpellet A/lösliches Protein; 3 Läufe mit Zellpellet B/inclusion bodies)). Evtl. auch Triton- X/Lysozym-Lyse wie in Woche 1 - Vorbesprechung (!) -» Nach der Lyse je ein 20 µl Aliqout für die Analyse durch SDS-PAGE abnehmen, 80 µl Wasser zugeben, mit 25 µl 5x Auftragspuffer versetzen und für 1 min aufkochen. Die Proben werden beschriftet (A1 und B1) und bei 20 C eingefroren. - Zellpellet B: 2 ml Lysat 30 min bei max rpm / 4 C in Eppendorf Tischzentrifuge zentrifugieren; bei Ansatz B vorher Tara des Zentrifugenröhrchens mit Deckel auf Feinwaage bestimmen! (zur späteren Bestimmung des inclusion body- Gewichtes).
23 Proteinfaltung 23 - Zellpellet A: etwa 5 ml des Cytosols (Überstand der Zentrifugation des aufgeschlossenen Zellpellets A) werden ausgegeben (dementsprechend erhalten sie Probe A1). - Vom Überstand» Probe für SDS PAGE nehmen: A2, B2 (wie A1 und B1 behandeln). - Vom Überstand» Jeweils 150 µl Probe entnehmen und in separaten Eppendorf-Reaktionsgefäßen bei 4 C für späteren Aktivitätstest aufheben: AL, BL Bei Ansatz A wird der lösliche Überstand direkt für die native Reinigung weiterverwendet und das Pellet verworfen. Bei Ansatz B wird der Überstand verworfen; aus dem Pellet werden die inclusion bodies präpariert. Für den 2. Tag werden 2 ml Ni-NTA-beads in 20% EtOH (entspricht 1 ml gepackten beads) in einem 15 ml Falcon-Röhrchen kurz abzentrifugiert. Der Überstand wird vorsichtig abgenommen und verworfen. Die Ni-NTA beads werden in 10 ml Puffer A10 gut resuspendiert, erneut abzentrifugiert und der Überstand wiederum verworfen. Anschließend werden die Beads in 10 ml frischem Puffer A10 resuspendiert und über Nacht bei 4 C äquilibriert. ACHTUNG: Beim Dekantieren / Abnehmen der Überstände stets darauf achten, dass keine beads verloren gehen!!! Die Dialyseschläuche, zweimal 8-10 cm, für die Dialyse am Ende des 2. Tages müssen über Nacht bei 4 C in Puffer F eingeweicht werden.
24 Proteinfaltung Tag (Mittwoch) Am Mittwochmorgen werden die Zellpellets A aufgeschlossen (siehe Dienstag), die zur nativen Aufreinigung verwendet werden. Diese stets auf Eis aufbewahren. Während des Aufschlusses der Zellpellets A kann die IB-Präparation fortgesetzt werden. Die endgültige denaturierende Proteinreinigung an den Ni-NTA beads muss nach der nativen Reinigung erfolgen. Reinigung der nativen TEV Protease Bitte darauf achten, dass alle Puffer eiskalt sind und dass das zu reinigende Protein nur möglichst kurz Raumtemperatur ausgesetzt ist. - die äquilibrierten (Puffer A10) Ni-NTA-beads in 15 ml Falcon tube abzentrifugieren, den Puffer verwerfen - Überstand von Lysat A auf beads geben, mischen, unter häufigem oder kontinuierlichem Mischen 30 min auf Eis inkubieren (evtl. Orbitalschüttler im Kühlschrank/mit Eis verwenden). - beads abzentrifugieren und Überstand (ohne Verlust von beads) vorsichtig abnehmen und zur Sicherheit zunächst noch auf Eis aufbewahren, Die TEV Protease sollte an die beads gebunden haben;» Probe für SDS-PAGE vom Überstand nehmen: A3 (wie A1 behandeln) - beads zweimal mit je 10 ml Puffer A10 waschen; Überstand verwerfen - beads zweimal mit je 10 ml Puffer A20 waschen; Überstand verwerfen -» Probe vom ersten A20 Waschschritt für SDS-PAGE nehmen: A4 (wie A1 behandeln) - Beads in verbliebenem restlichen Überstand resuspendieren und in 5ml-Polypropylen-Leersäule überführen; Durchfluss verwerfen. Bitte beachten, daß der verbleibende Überstand komplett aus der Säule abläuft, diese jedoch nicht trockenläuft! - 4 ml Puffer A250 vorsichtig über die beads schichten (Aufwirbelung der beads vermeiden!!!) und das Eluat in 8 Fraktionen zu je 500 µl auffangen - Um die Peak-Fraktionen zu bestimmen, werden aus jeder Fraktion einige µl zu je 0.1 ml verdünntem Bradford-Reagens gegeben. Eine tiefblaue Farbe zeigt große Proteinmengen an. Die Peak-Fraktionen werden vereinigt und enthalten
25 Proteinfaltung 25 die gereinigte TEV Protease;» Probe für SDS PAGE nehmen: A5 (wie A1 behandeln) - Nachdem das Protein vollständig eluiert wurde, beads für die denaturierende Reinigung aus Inclusion Bodies in 5 ml Puffer B resuspendieren und in das 15 ml Falconröhrchen überführen. Anschließend abzentrifugieren, Überstand verwerfen, in 10 ml Puffer B resuspendieren und erneut abzentrifugieren. Der Überstand wird wiederum verworfen (Waschschritt) und die beads in 10 ml frischem Puffer B resuspendiert und unter gelegentlichem Mischen äquilibriert. Leersäule spülen und aufbewahren (wird wiederverwendet)! Die native TEV Protease wird im 2. Dialyseschritt (über Nacht) parallel zur denaturierten TEV Protease gegen Puffer F ( = Lagerungspuffer) dialysiert und solange auf Eis aufbewahrt. IB Präparation und Reinigung - Pellet von Lysat B in 1.9 ml Puffer A10 durch vortexen resupendieren.» Probe für SDS PAGE nehmen: B3 (wie B1 behandeln) - 15 min bei 14000rpm/4 C in Eppendorf Tischzentrifuge zentrifugieren - Pellet in 1.9 ml Puffer A10 und 1% Triton X100 (100µl) resuspendieren min/14000rpm/4 C in Eppendorf Tischzentrifuge zentrifugieren» Probe vom Überstand für SDS PAGE nehmen: B4 (wie B1 behandeln) - Pellet in 1.7 ml Puffer A ml Puffer B resuspendieren min/14000rpm/4 C in Eppendorf Tischzentrifuge zentrifugieren» Probe vom Überstand für SDS PAGE nehmen: B5 (wie B1 behandeln) Die gereinigten IB s befinden sich im Pellet. Das Nassgewicht der IB s wird für jeden Reinigungsschritt auf der Feinwaage bestimmt. Gereinigte IB s können ggf. bei 4 C über Nacht gelagert werden Was stellen Sie fest? Achtung: Vor Beginn das Leergewicht des Zentrifugenröhrchens bestimmen!!!
26 Proteinfaltung 26 Solubilisierung der IBs und denaturierende Proteinreinigung Bitte darauf achten, dass Puffer B, C, D und E Raumtemperatur haben. - die gereinigten IB s in 1.9 ml Puffer B (Raumtemperatur) resupendieren und (bei 65 C im Wasserbad/Thermoschüttler) vollständig solubilisieren - gelöste IB s 15 /14000rpm/4 C in Eppendorf Tischzentrifuge zentrifugieren, Überstand sofort in ein 15 ml Falconröhrchen überführen.» Probe für SDS PAGE nehmen: B6. Aufgrund des hohen Guanidiniumhydrochlorid- Gehaltes NICHT direkt in 5x Auftragspuffer aufkochen, sondern zunächst 25 µl bei 20 C frieren! Vor dem Auftrag wird ein 5 µl Aliquot entnommen, 1:10 mit Wasser verdünnt, mit einem geeigneten Volumen 5x Auftragspuffer versetzt und für 1 min aufgekocht. - 5 ml Puffer B zu gelösten IB zugeben um das Volumen zu vergrößern. Überstand auf die in Puffer B äquilibrierten Ni-NTA-beads geben, mischen, und unter häufigem oder kontinuierlichem Mischen 30 min bei Raumtemperatur inkubieren (evtl. Orbitalschüttler benutzen) - beads abzentrifugieren, Überstand vorsichtig dekantieren und aufbewahren;» Probe für SDS-PAGE nehmen: B7. Wie B6 behandeln! - beads zweimal mit 10 ml Puffer C (Raumtemperatur) waschen; Überstand verwerfen; dabei wird vom Solubilisierungsmittel Guanidiniumhydrochlorid zu Harnstoff gewechselt, das die Faltung während der Dialyse begünstigt - beads mit 10 ml Puffer D (ph = 6.3, Raumtemperatur) waschen; Überstand verwerfen;» Probe für SDS-PAGE nehmen: B8. Wie B6 behandeln! - beads erneut kurz zentrifugieren und den restlichen Überstand KOMPLETT abnehmen. Bitte beachten Sie, daß kein restlicher Überstand verbleibt, der Puffer E für den folgenden Elutionsschritt wird sonst zu stark verdünnt! - 5 ml Puffer E (ph = 4.5, Raumtemperatur) zu den beads zugeben, komplett mischen und 5 min bei RT einwirken lassen. - Die beads erneut abzentrifugieren und Überstand komplett abnehmen, enthält die denaturierte TEV Protease. - Nachdem das Protein eluiert wurde, beads für die weitere Verwendung 1 x in 10 ml A250 und dann 2 x in je 10 ml frischem 1 x Puffer H resuspendieren, abzentrifugieren und den Überstand verwerfen. (Achtung: Intensives Waschen der beads ist wichtig, um alle Harnstoff- Spuren von Puffer E zu entfernen!!!)
27 Proteinfaltung 27 - beads erneut in 10 ml frischem 1 x Puffer H resuspendieren, unter gelegentlichem Mischen äquilibrieren und über Nacht bei 4 C aufbewahren. Die denaturierte TEV Protease befindet sich jetzt in 5 ml Puffer E;» Probe für SDS PAGE nehmen: B9. Wie B6 behandeln. Rückfaltung durch Dialyse - Die denaturierte, in 6M Harnstoff gelöste TEV Protease in Puffer E ganz vorsichtig unter Rühren mit 1M NaOH auf ph 8.5 bringen. Zur ph- Bestimmung ph-farbstreifen verwenden. Bitte ph zu Beginn der Titration notieren. - Die Lösung in einen Dialyseschlauch füllen und gegen 2 x 3000 ml (gesamter Kurs) eiskalten Puffer F dialysieren: 1x 2 Stunden, dann noch 1x über Nacht (Die native TEV-Protease wird im zweiten Schritt ebenfalls zugeben.) 3. Tag (Donnerstag) Rückfaltung durch Dialyse Teil II - Nach der Dialyse in der gekühlten Tischzentrifuge in 2 ml Eppendorfröhrchen für 15 bei rpm/4 C zentrifugieren, um das Präzipitat abzutrennen. Das gefaltete Protein befindet sich im Überstand, welcher sofort nach der Zentrifugation vom Pellet vorsichtig abgenommen wird. Volumen des Überstandes bestimmen.» Von Überstand und Präzipitat jeweils Probe für SDS PAGE nehmen: B10, B11. Das gesamte Präzipitat wird hierzu im demselben Volumen von Wasser möglichst homogen resuspendiert, das für den Überstand zuvor gemessen wurde (ca. 3 ml). Sowohl vom Überstand als auch von der Suspension 40 µl Probe entnehmen mit 60 µl Wasser und 25 µl 5x Auftragspuffer versetzen und1 min aufkochen. Bestimmung der Proteinkonzentration nach Bradford Dieser Proteintest beruht auf der Beobachtung von Bradford (1976), wonach das Absorptionsmaximum einer sauren Lösung von Coomassie Brilliant Blau G-250 nach Ausbildung von Proteinkomplexen von 465 nm nach 595 nm verschoben wird. Bei geeigneter Wahl von Protein- (1-25 µg/ml) und Farbstoffkonzentration besteht ein nahezu linearer Zusammenhang zwischen der Absorption bei 595 nm und dem Proteingehalt der Lösung. Zunächst wird eine Eichkurve mit einem Protein (bovines Serumalbumin, BSA) bekannter Konzentration erstellt. Dazu werden 6 unterschiedliche Mengen BSA in einem konstanten Volumen mit der Farbstofflösung
28 Proteinfaltung 28 gemischt. Nach 5-minütiger Inkubation bei RT wird die Extinktion bei 595 nm gegen den Leerwert (Farbstofflösung ohne Protein) bestimmt. Nach Messen der Proteinprobe kann aus der Eichgerade unter Berücksichtigung der Verdünnung der Proteingehalt bestimmt werden. Protokoll Bradford-Assay im Anhang. Falls Sie inder Vorwoche (Teil Dr. B. Beatrix) schon eine Eichgerade für den Assay erstellt haben, kann diese weiterverwendet werden aber bitte mit einer Testmessung überprüfen (!). Protokoll für Bradford Eichgerade siehe Anhang. Aufgabe: Berechnen Sie jeweils für Präparation A und B aus Konzentration und Volumen die Ausbeute (im mg) der Reinigung! Vergleichen Sie diese Werte mit der Menge an TEV-Protease in Ihren Zellpellets und geben Sie die Ausbeute ebenfalls in Prozent an. Vergleichen Sie auch die Proteinkonzentration in den Rohlysaten AL und BL. Die Bestimmung der TEV-protease Konzentration (sauberes Protein, Überstand nach Dialyse) kann auch über die UV absorption erfolgen. Dabei entspricht 1 OD(280nm)=1.19mg/ml ACHTUNG: Beachten Sie, in welcher Form die TEV-Protease bei beiden Präparationen ursprünglich vorlag!!! SDS PAGE zur Kontrolle der beiden Reinigungen 12% SDS-PAGE Minigele mit 15 Taschen werden nach Anweisung der Betreuer gegossen (Dienstag). Die Proben der vergangenen Tage (außer A4, B8) in die Taschen des Gels füllen: MW: 10 µl - Molekulargewichtsmarker A1: 5 µl - Gesamtheit aller Zellbestandteile A2: 5 µl - Lösliche Proteine A3: 5 µl - Nicht an Ni-NTA gebundene Proteine A5: 5 µl - Peak-Fraktion Ni-NTA-Eluat B1: 5 µl - Gesamtheit aller Zellbestandteile B2: 5 µl - Lösliche Proteine B3: 5 µl - Nicht lösliche Proteine (Zellpellet) B4: 10 µl - Überstand der Triton X-100 Resuspension B5: 10 µl - Überstand der A10/B Resuspension B6: 10 µl - Solubilisierte IB s / Auftrag Ni-NTA B7: 10 µl - Nicht an Ni-NTA gebundene Proteine B9: 10 µl - Eluat Ni-NTA Säule B10: 10 µl - Überstand der Dialyse B11: 10 µl - Pellet der Dialyse ACHTUNG: Von den Proben B4-B9 soll möglichst viel aufgetragen werden, jedoch dürfen die Taschen nicht ineinander laufen. Bitte entsprechend weniger laden, falls sich z.b. nur 20 µl sicher auftragen lassen sollten.
29 Proteinfaltung 29 Laufbedingungen: V. Elektrophorese beenden, kurz bevor der Blaumarker aus dem Gel läuft. Färben: mind min in Coomassie Färbelösung schwenken (Abzug!), dann in Entfärber schwenken, bis alle Banden gut sichtbar sind (Abzug!) Die TEV Protease hat ein Molekulargewicht von ca. 27kDa. Aufgabe: Zeichnen sie schematisch den Ablauf beider Reinigungsvorschriften und ordnen Sie die Proben des SDS-Gels zu. Identifizieren Sie die TEV- Protease im SDS-Gel. Beurteilen Sie den Reinheitsgrad, Reinigungsverlauf und Ausbeute der beiden Präparationen! Vergleichen Sie hierzu auch Pellet und lösliches Protein nach erfolgter Rückfaltung (Proben B10 & B11)! Wie effizient war die Rückfaltung durch Dialyse? Aktivitätstest Mit der gereinigten TEV Protease wird von einem Fusionsprotein das N-terminale Hilfspeptid abgespalten. Das Fusionsprotein wurde erstellt, um die effiziente und schnelle Reinigung des Zielproteins durch Fusion mit einem Histidin-Tag (ähnlich wie bei der im ersten Versuchsteil gereinigten TEV-Protease) zu ermöglichen. Durch Schneiden gleicher Mengen an Fusionsprotein (Substrat) sowohl mit verschiedenen Mengen an gereinigter TEV-Protease als auch mit den Rohlysaten soll die Aktivität der verschiedenen Präparationen abgeschätzt werden. In einem weiteren Versuch soll das Reaktionsgemisch des Verdaus mit Ni-NTA inkubiert werden. Die Proben werden mittels SDS-PAGE auf Proteolyse des Zielproteins untersucht. TEV-Aktivitätstest: Bereiten Sie die folgenden Reaktionsansätze vor: Probe Nr Fusionsprotein (2.2 mg/ml) / [µl] x Puffer G / [µl] x Puffer G2 / [µl] TEV nativ / [µg] - 2,0 0,5 0,1 0, ,0 TEV rückgefaltet / [µg] ,0 0,5 0,1 0, Rohlysat TEV nativ / [µg] ,0 0, Rohlysat TEV IB / [µg] ,0 0,1 - H 2O / [µl] 2 ad 15 ad 15 ad 15 ad 15 ad 15 ad 15 ad 15 ad 15 ad 15 ad 15 ad 15 ad 15 ad 45 Ansätze mischen und 60 min bei 34 C inkubieren. Proben 1 13 werden sofort nach der Ende der Reaktion mit 5 µl 5x SDS-PAGE Probenpuffer versehen, aufgekocht und bis zum Laden des Gels bei RT aufbewahrt. Die verschiedenen Reaktionen sollen möglichst gleichzeitig gestartet werden
30 Proteinfaltung 30 Zugabe der Protease entsprechend koordinieren. Sind Proteinkonzentrationen zu niedrig um die entsprechende Menge TEV-Protease in einem Volumen von 2 µl pipettieren zu können, kann das Ansatzvolumen vergrößert werden. Während des Verdaus werden die in Puffer H äquilibrierten Ni-NTA Beads abzentrifugiert, der überstehende Puffer komplett abgenommen. Eventuell farblos gewordene beads oder sonstige Verunreinigungen ebenfalls mit abnehmen. Zu den verbleibenden Beads wird ein möglichst gleiches Volumen an Puffer H zugegeben und gevortext. Von den resuspendierten Beads werden 200 µl abgenommen, in ein Eppendorf Reaktionsgefäß überführt und erneut abzentrifugiert. Der überstehende Puffer wird wiederum möglichst komplett abgenommen. Nach Beendigung des Verdaus werden die 45 µl Reaktionsmix von Probe 14 zu den so vorbereiteten beads gegeben, gevortext und die Mischung für 15 min unter stetigem Mischen (Schüttler!!!) bei Raumtemperatur inkubiert. Anschließend wird wiederum abzentrifugiert, 20 µl des Überstandes abgenommen, mit 5 µl SDS-PAGE Probenpuffer versetzt und aufgekocht. In der Zwischenzeit SDS-PAGE vorbereiten (15% Polyacrylamid, 15 Taschen). Alle 14 Proben auf das Gel laden (Jeweils 10 µl; Molekulargewichtsstandard nicht vergessen!). Laufbedingungen etc. s.o. Aufgabe: Ordnen Sie die Banden auf dem Gel dem Fusionsprotein, seinen Fragmenten sowie der TEV-Protease zu. Die Proteaseaktivität soll anhand der Abnahme des Vollängenproduktes und der Zunahme der Fragmente abgeschätzt werden. Vergleichen Sie die Aktivität der gereinigten Fraktionen beider Expressionen untereinander und mit denen der Rohlysate. Vergleichen Sie die Reinheit des Zielproteins in Probe 2 (Spaltung durch native TEV) und 14 (zusätzliche Inkubation mit Ni-NTA). Diskutieren Sie die Unterschiede. ACHTUNG: Eventuell notwendige Berechnungen nachvollziehbar darlegen!!! Keine genaue Berechnung der MW s im Gel über die gemessene Laufstrecke etc. nur eine Abschätzung anhand des Markers vornehmen. Molekulargewichte: TEV-protease kda Fusionsprotein(eGFP) ca. 39 kda natives Protein ohne His-Tag ca. 36 kda Tag plus Linker ca. 3 kda (läuft auf dem Gel deutlich größer und wird nur schwach gefärbt!!!) Die Zentrifugenröhrchen und die 5ml Säulen werden wiederverwendet und eingesammelt.
31 Proteinfaltung 31 Fusionsprotein: Fusionsprotein aus petm11-sumo3gfp Histag - TEV-site - SUMO3- EGFP 39 kda Gesamtgröße 3 kda Histag (werden abgeschnitten - läuft größer, aber Gel nicht bis zum ende laufen lassen) 36kDa SUMO3-eGFP
32 Proteinfaltung Tag (Freitag) Versuch 3. Fluorescence Thermal Shift Assay (Differential Scanning Fluorimetry) Die Kenntnis über die Stabilität eines Proteins bzw. der Bedingungen in denen das Protein mit dem man arbeitet stabil ist, ist für eigentlich alle weiteren Experimente die man mit dem Protein durchführen möchte essentiell. Beispielsweise sollten für Aktivitätsexperimente aber auch Lagerung und Aufreinigung des Proteins Pufferbedingungen gewählt werden, die die Stabilität positiv beeinflussen. Die bessere Faltung eines Proteins hat auch direkt auswirkungen auf z.b. die Kristallisierbarkeit von Proteinen und Protein-Komplexen deswegen werden Proteine routinemäßig in verschiedenen Puffersystemen getestet. Es wurde bereits eine Methode im Praktikum vorgestellt (Entfaltung von egfp, Tag 1) bei dem in einer Titration mit einem Denaturierungsmittel untersucht wurde, wie stabil egfp ist. Das System hat mehrere Einschränkungen, die es als Hochdurchsatzmethode nicht anwendbar machen: Zum einen fluoresziert nicht jedes Protein so intensiv wie egfp, man müsste also auf ein anderes Signal wie z.b. CD- Spektroskopie zurückgreifen um zu erkennen ob das Protein gefaltet ist und zum anderen ändert sich natürlich bei einer Titration mit GuaHCl die Pufferumgebung des Proteins und macht also zum Screenen von Pufferbedingungen keinen Sinn. Als Methoden, die ohne denaturierende Zusätze auskommt, bietet sich die Untersucheung der thermischen Stabilität des Proteins an, bei dem sog. Schmelzkurven aufgenommen werden. Dabei wird das Protein langsam (z.b. 30 K/h) erhitzt und gleichzeitig gemessen. Als Signal kann z.b. die Faltung des Proteins direkt mit Circulardichroismusmessungen beobachtet werden (CD-Schmelzen) oder auch in kalorimetrischen Messungen die Änderung der Temperatur bei konstanter Heizrate von Protein und einer Referenz verfolgt werden, bzw der gemessen wir wieviel Energie man benötigt um eine Probe bzw. die Referenz auf eine Temperatur zu bringen (Differential Thermal Analysis, DTA; Differential Scanning Calorimetry, DSC). Ein Beispiel für eine solche kalorimetrische Messung zeigt Abb. 10. In der Praxis würden also z.b. DSC-Kurven des selben Proteins in verschiedenen Pufferbedingungen miteinander verglichen. Leider hat die Methode relativ viele Einschränkungen zum einen braucht man ein Kalorimeter, zum anderen wird bei jedem Versuch sehr viel Protein benötigt. Die Messung der zugeführten Wärme, bzw. der Temperatuunterschiede Referenz vs. Protein ist zudem auch technisch recht aufwendig. Die größte Einschränkung ist jedoch (wie auch beim CD-Schmelzen), dass man nur eine Bedingung pro Experiment testen kann und sich die Methode daher nicht zum Hochdurchsatz-Screenen eignet.
33 Proteinfaltung 33 Abbildung 10: Typische Schmelzkurve eines Proteins in einer DSC-Messung. Im Schmelzbereich wo das Protein kooperativ schmilzt muss mehr Wärme zugeführt werden um die Temperatur zu erhöhen als im gefalteten (oder komplett ungefalteten) Zustand. Der Peak im DSC entspricht dem Schmelzpunkt des Proteins (Quelle: Eine sehr elegante und relativ einfache Methode, die es erlaubt gleichzeitig bis zu 96 (oder sogar 384) verschiedene Bedingungen zu testen ist der Fluorescence Thermal Shift Assay (Differential Scanning Fluorimetry, oft auch Thermofluor genannt). Dabei wird das Protein in Gegenwart eines Fluoreszenzfarbstoffs erwärmt (z.b. ANS oder SYPRO Orange). Denaturiert das Protein, kann sich der Farbstoff an hydrophobe Bereiche (die normalerweise im protein-kern liegen) anlagern. Durch diese Umgebungsänderung erhöht sich die Fluoreszenzintensität (Abb11.). Abbildung 11: Änderung der Fluoreszenzintensität des Fluoreszenzfarbstoffs bei anlagerung an hydrophobe Bereiche im denaturiereten Protein. Rechts: SYPRO-Orange Farbstoff und Spektren (Ex/Em Spektren) Ein DSF-Experiment verläuft analog zu jedem anderen Schmelzexperiment indem man die Fluoreszenz des verwendeten Farbstoffs bei langsamer Erhöhung der Temperatur beobachtet. Der Vorteil liegt dabei zum einen in der genaueren Detektion
34 Proteinfaltung 34 von Fluoreszenz (im vgl. zu Wärmemenge wie bei DSC) und der massiven Parallelisierbarkeit des Assays. Man kann zum Beispiel 96-well Platereader mit Heizfunktion (wie z.b. im egfp-versuch verwendet) oder einfach ein Realtime-PCR Gerät verwenden, was den Vorteil hat, dass man noch geringeren Probenvolumina braucht. Eine Realtime-PCR für qpcr wird sozusagen als Heiz-Fluoreszenz- Detektor zweckentfremdet indem keine Zyklen wie bei einer PCR gefahren werden, sondern lediglich ein anderes Programm verwendet wird bei dem langsam ein Temperaturgradient gefahren wird und nebenbei die Fluoreszenz der einzelnen PCR- Gefäßen gemessen wird. Abbildung 12: Schmelzkurve im TSA (Protein Expr. and Purif. 91 (2013) ) Unterschiede in der Stabilität des Proteins bei verschiedenen Puffer-Bedingungen (ph, Salz, Ionen, Glycerin,.) zeigen sich direkt in einer Änderung des Schmelzverhaltens des Proteins (Beispiel siehe Abb 13).
35 Proteinfaltung 35 Abbildung 13: Beispiel für TSA-Messung (Pufferscreen). Effekt von Puffersubstanz und ph auf die Stabilität von Glucose-isomerase. (Protein Expr. and Purif. 91 (2013) ) Versuch: Im Praktikum soll die Stabilität eines Testproteins (α-lactalbumin) bei verschiedenen Pufferbedingungen untersucht werden. Es steht eine 96-well Realtime-PCR für das Experiment zur Verfügung, bei 12 Gruppen kann also jede Gruppe einen 8er-Slot verwenden. Bitte sprechen Sie sich mit Ihren Kommilitonen ab und versuchen Sie möglichst viele Bedingungen zu testen. Stellen sie die zugehörigen Pufferlösungen her (kleiner Maßstab! Pro Ansatz braucht man weniger als 50µl trotzdem bitte 1ml der jeweiligen Test-Puffer herstellen, da sonst der Pipettierfehler zu groß wird. Pipettierschema pro Ansatz (bitte auf Eis in Eppis pipettieren, der Reihe nach und am Ende ganz vorsichtig mit der Pipette mischen) +40µl Test-Puffer + 4µl SYPRO-Orange (verdünnt) + 3µl Protein (α-lactalbumin 5mg/ml)
36 Proteinfaltung 36 Beispiel: Gruppe 1 möchte die Stabilität des Proteins in Abhängigkeit der NaCl-Konzentration messen, z.b. in 20mM Tris ph8.0 mit NaCl-Konzentrationen bis 1.5M. [NaCl] M Tris ph 8.0 NaCl- 5M Stocklösung [µl] 1M Tris ph8- Stocklösung [µl] Wasser [µl] mm mm mm mm mm mm mm mm Vorschläge für weitere Reihen: Salz wie oben, aber ph 5, 6, (welcher Pufferbereich? ) 7 und 9 (Tris) Imidazol in Tris ph 8 ( 500mM, 400mM, 300mM, 200 mm, 150mM, 100mM 50mM, 0 mm) Glycerin in Tris ph 8 (0-10% v/v) Guanidiniumchlorid (0-4M) (NaCl, Tris ph8.0) Harnstoff (0-4M) (NaCl, Tris) Verschiedene Puffersubstanzen (MES, HEPES, Phosphat) und NaCl Bitte sprechen Sie sich mit Ihren Kommilitonen ab und kommunizieren Sie auch Ihre Pufferbedingungen zu den anderen für die Auswertung benötigen Sie alle Informationen von allen 96 wells. Bitte pipettieren Sie die unterschiedlichen 40µl-Ansätze am Platz (gekühlt?) im Eppendorf tube vor, mischen vorsichtig und geben dann je 20µl in die 96well-PCRplatte an die Ihrer Gruppe zugehörigen Plätze:
37 Proteinfaltung 37 Der Thermal-Shift Assay läuft ca. 1.5h. Die Ergebnisfiles können mit der Biorad- Software geladen und z.b. nach MS Excel exportiert werden. Die Bio-Rad Software ist im Rahmen des Praktikums frei installierbar und auch zur Auswertung zu Hause freigegeben. Aufgaben: 1. Versuchen Sie möglichst viel über das Protein zu erfahren: Datenbank- Recherche etc. Molekulargewicht, molarer Extinktionskoeffizient, Isoelektrischer Punkt etc. Hat es eine Funktion? Bitte schreiben Sie keine Doktorarbeit über das Protein, eine Stichpunktliste (mit Quelle) der wichtigsten Eigenschaften (s.o.) reicht völlig. Das ist vor allem eine Übung für Sie. 2. Beschriften exemplarisch Sie an einer(!) ausgewählten Schmelzkurve die unterschiedlichen Zustände des Proteins bzw. des Fluorophors und beschreiben Sie kurz, was während des Schmelzens passiert. Warum ist die Grundfluoreszenz bei niedrigen Temperaturen oft schon recht hoch und sinkt dann während des Schmelzens ab? 3. Stellen Sie die Schmelzkurven für die Bedingungen aller Gruppen grafisch dar (F vs. Temp, sowie die Ableitung). Am einfachsten wird es sein, wenn Sie die exportierten Daten in Excel auswerten. Plotten Sie Für alle verwendeten Reihen Schmelzpunkt vs. Bedingung also z.b. [NaCl] oder ph. Bitte überprüfen ob der jeweilige Tm sinnvoll ist, automatische Auswertungen sind nicht verlässlich. 4. Welche Bedingungen sind eher stabilisierend und welche nicht? Gibt es deutlich Trends? Plotten Sie exemplarisch z.b. die Abhängigkeiten des Temperaturshifts von der NaCl-Konzentration oder z.b. Pufferkomponenten etc. (je nachdem, ob klare Trends erkennbar sind). 5. Gibt es einen Zusammenhang zwischen Stabilität des Lactalbumins und der Imidazol-Konzentration? Falls ja: Was bedeutet das für die Aufreinigung von His 6 -getaggten Proteinen?
38 Proteinfaltung 38 ANHANG 1: Bradford Proteinbestimmung - Eichgerade Standard: BSA (Thermo Scientific) 2 mg / ml in ddh 2 O (wird ausgeteilt) Verdünnen Sie den BSA Standard so mit Wasser, dass Sie 4 ml mit einer Konzentration von 0,02 µg/µl erhalten. x µl + y ml ddh 2 O = 4 ml Konzentration = 0.02 µg / µl = BSA Stamm-Lösung Wie kann man dieses Volumen H 2 O möglichst genau abmessen? Diese BSA Stammlösung stellen Sie 2 x her!! (unabhängige Verdünnungen) Nummerieren Sie 2 x 11 Eppendorf tube (1,5 ml). Mischen sie zunächst die BSA Stammlösung und H 2 O in den Epis. Geben sie die konzentrierte Bradfordlösung zu einer Probe und mischen Sie die Probe sofort durch Vortexen. Danach verfahren sie genauso mit der nächsten Probe. Anschliessend inkubieren sie alle Proben 5 min im Dunkeln (Timer). Überführen Sie 300 µl jeder Probe in eine 96-well Platte (Beschriftung). Vermeiden Sie die Entstehung von Luftblasen dabei. Sollten sich dennoch Luftblasen bilden, können sie diese direkt vor der Messung mit einer Kristallspitze (1-10 µl) entfernen (der freundliche Assistent am Platereader hilft auch). Messen sie ihre Proben bei 595 nm am Platereader (mit Hilfe eines Assistenten). Das Gerät erstellt automatisch eine Excel-Tabelle für Sie. Probe µl BSA stock µl ddh 2 O Bradford Lösung total Protein (µg) Vortexen Sie die Probe direkt nach Zugabe der Bradfordlösung 0 0
39 Proteinfaltung 39 Erstellen sie eine Eichgerade mit Excel. Tragen sie zunächst beide Messreihen unterscheidbar (z.b. farbig) auf. Diskutieren Sie das Ergebnis mit einem Assistenten. Wenn Ihre Eichgerade verwendbar ist, fahren Sie fort mit Ihren eigenen Proben. Für das Protokoll bereiten Sie eine beschriftete (!) Eichgerade aus den Mittelwerten mit Standardabweichung vor. Testen sie eine Verdünnung ihrer Probe mit der Bradford-Lösung auf eine ähnliche Blauverfärbung wie bei den Standards. Es kann durchaus sein, dass man eine Probe 1:100 oder mehr verdünnen muss, um im Breich der Eichgeraden zu liegen. Machen sie zwei unabhängige, genaue Verdünnungen ihrer Probe (x / 2x) und bestimmen sie die Konzentration anhand ihrer Eichgeraden durch 2 Messungen jeder der beiden Verdünnungen. Wenn ihr Messwert nicht im mittleren Bereich ihrer Eichgerade liegt, wiederholen Sie die Proteinbestimmung mit Ihren Probe einer besser geeigneten Verdünnung. In Ihr Protokoll gehören die Originalmessdaten und alle Berechnungen ihrer Werte. Achten Sie auch korrekte Einheiten!! Anhang 2: Verwendeter Proteinmarker für SDS-Gele Unstained Protein Molecular Weight Marker (Fermentas)
40 Proteinfaltung 40 Protokoll BC2: Proteinfaltung und -missfaltung in vivo und in vitro Name: Sheldon Cooper Fach: quantum physics Matr.-Nr.: Gruppen-Nr.: 42 Gruppenmitglieder: Leonard Hofstadter Kurs: xxx-yyy Einführung zum Thema der Kurswoche: Was ist Proteinfaltung und welche Rolle spielt diese in vitro und in vivo. Führen Sie die 3 Ansätze an und stellen Sie diese in Methoden und Zielen gegenüber (1 Seite) Versuch 1: Denaturierungskurve egfp Einleitung: Kurze Einleitung zur Denaturierung. Was wird im Versuch mit welcher Methode gemacht und warum? Was ist das Ziel des Versuchs. (1 Seite) Durchführung: - Versuchsdurchführung nicht extrem ausführlich aber nachvollziehbar - Ergebnisse: 1. Vorexperiment: Plot Fluoreszenz vs. [GuaHCl] für beide Temperaturen, begründung welchen Bereich Sie näher untersuchen 2. Denaturierungskurve - Plot Fluoreszenzintensität vs. [GuaHCl] - normierter Plot %gefaltet vs. [GuaHCl] [GuaHCl] - Für den Übergangsbereich tabellarisch K d [GuaHCl] G und G (mathematisch) auf - Plot: [GuaHCl] G vs. [GuaHCl], extrapolation von [GuaHCl]=0M, Gleichung angeben. - berechnen G pro Rest des Proteins. Diskussion: Ist egfp ein typisches Protein oder besonders stabil/instabil? Ist die Annahme gerechtfertigt dass es sich um einen Alles-oder-nichts-Übergang handelt? Versuch 2: Expression, Reinigung und Renaturierung von rekombinanter Tobacco Etch Virus (TEV) Protease Einleitung: Kurze Einleitung zur heterologen Expression und evtl. Problemen (z.b. Inclusion bodies). Was wird im Versuch mit welcher Methode gemacht und warum? Was ist das Ziel des Versuchs. (1 Seite)
41 Proteinfaltung 41 Durchführung: - Pufferberechnung ( nur die Puffer die die Gruppe hergestellt hat) - Versuchsdurchführung nicht extrem ausführlich aber nachvollziehbar (Proben angeben A1, A2, etc), bitte auch z.b. schreiben wie die Elution des Proteins bei A+B funktioniert falls das nicht schon in der Einleitung passiert ist. Es ist sinnvoll die Durchführung nicht verschachtelt sondern getrennt für A und B zu schreiben. (3 Seiten; Schema als Anhang) Ergebnisse: - Reinigungsgel, beschriften, diskutieren (die Molekulargewichte anhand des Markers abschätzen, keine exakte Berechnung nötig) - Konzentrationsbestimmung mit Rechnung! / Bradford Gerade von vorheriger Woche / ungefähre Ausbeuteberechnung in mg & % - Aktivitätstest: Was wurde pipettiert, bitte mit Rechnung, Gel, beschriften, diskutieren (max. 5 Seiten) Diskussion: Welche Schlussfolgerungen sind aufgrund der Ergebnisse möglich? Wie gut wurde der Versuch durchgeführt und inwieweit wurden die Erwartungen erfüllt? Was bedeuten die Ergebnisse? Vergleich Reinigung nativ / IB+ Rückfaltung und Aktivität der TEV aus A und B (2 Seiten) Versuch 3: Thermal Shift Assay Einleitung: Prinzip des Thermal Shift Assays kurz erklären und warum man das macht. Durchführung: Versuchsdurchführung nicht extrem ausführlich aber zumindest nachvollziehbar (und Abweichungen vom Skript) (max. 1 Seite). Ergebnisse: Ergebnisse graphish (12 plots) siehe auch Fragen zum Versuch. Diskussion: (Trends, Stabilität, Fragen, siehe oben) (max Seiten) WICHTIG: Den Umfang des Protokolls zur 2. Woche gering halten. Bitte die angeführten 25 Seiten (12pt Schrift, 1.5xfacher Zeilenabstand) als Obergrenze festlegen. Kurze, wissenschaftlich prägnante Protokolle werden definitiv besser bewertet als ausschweifende, literarische Texte.
Anwendungsbericht zur Herstellung des Proteins GST-GFP-NLS
 Anwendungsbericht zur Herstellung des Proteins GST-GFP-NLS Von: Andreas Tschammer, Fachhochschule Aalen-Hochschule f. Technik und Wirtschaft, Fachbereich Chemie, Schwerpunkt Molekulare Biotechnologie Material
Anwendungsbericht zur Herstellung des Proteins GST-GFP-NLS Von: Andreas Tschammer, Fachhochschule Aalen-Hochschule f. Technik und Wirtschaft, Fachbereich Chemie, Schwerpunkt Molekulare Biotechnologie Material
Plasmidisolierung. Mit Plasmiden können Sie Gene in Organismen einschleusen und so deren Eigenschaften verändern.
 Plasmidisolierung Mit Plasmiden können Sie Gene in Organismen einschleusen und so deren Eigenschaften verändern. Was können Sie lernen? Sie lernen eine ringförmige DNA, ein Plasmid, zu isolieren. Mit diesem
Plasmidisolierung Mit Plasmiden können Sie Gene in Organismen einschleusen und so deren Eigenschaften verändern. Was können Sie lernen? Sie lernen eine ringförmige DNA, ein Plasmid, zu isolieren. Mit diesem
SDS Polyacrylamidgelelektrophorese (SDS-PAGE) Mini-Gelträger nach Anleitung zusammenbauen. Saubere Handschuhe tragen!!!
 aktualisiert, 08.03.2011, Wera Roth1 SDS Polyacrylamidgelelektrophorese (SDS-PAGE) Anleitung für Minigele Mini-Gelträger nach Anleitung zusammenbauen. Saubere Handschuhe tragen!!! Glasscheiben ordentlich
aktualisiert, 08.03.2011, Wera Roth1 SDS Polyacrylamidgelelektrophorese (SDS-PAGE) Anleitung für Minigele Mini-Gelträger nach Anleitung zusammenbauen. Saubere Handschuhe tragen!!! Glasscheiben ordentlich
Western Blot. Zuerst wird ein Proteingemisch mit Hilfe einer Gel-Elektrophorese aufgetrennt.
 Western Blot Der Western Blot ist eine analytische Methode zum Nachweis bestimmter Proteine in einer Probe. Der Nachweis erfolgt mit spezifischen Antikörpern, die das gesuchte Protein erkennen und daran
Western Blot Der Western Blot ist eine analytische Methode zum Nachweis bestimmter Proteine in einer Probe. Der Nachweis erfolgt mit spezifischen Antikörpern, die das gesuchte Protein erkennen und daran
Biochemisches Grundpraktikum. Elektrophoretische Trennung von Proteinen
 Biochemisches Grundpraktikum Versuch Nummer G-05 05: Elektrophoretische Trennung von Proteinen Gliederung: I. SDS-Polyacrylamid-Gelelektrophorese... 2 a) Versuchsziele, Aufgaben... 2 b) Versuchsdurchführung...
Biochemisches Grundpraktikum Versuch Nummer G-05 05: Elektrophoretische Trennung von Proteinen Gliederung: I. SDS-Polyacrylamid-Gelelektrophorese... 2 a) Versuchsziele, Aufgaben... 2 b) Versuchsdurchführung...
Praktikum Biochemie Einführung in die Molekularbiologie. Bettina Siebers
 Praktikum Biochemie Einführung in die Molekularbiologie Bettina Siebers Rekombinante Expression einer Esterase aus Pseudomonas aeruginosa in E. coli Polyacrylamide Gelelektrophorese (PAGE) Denaturierende
Praktikum Biochemie Einführung in die Molekularbiologie Bettina Siebers Rekombinante Expression einer Esterase aus Pseudomonas aeruginosa in E. coli Polyacrylamide Gelelektrophorese (PAGE) Denaturierende
GEBRAUCHSANLEITUNG. Glutatione Agarose Resin
 GEBRAUCHSANLEITUNG Glutatione Agarose Resin Agarose zur Affinitätsreinigung von GST-Tag-Fusionsproteinen und anderen Glutathion-Bindungsproteinen (Kat.-Nr. 42172) SERVA Electrophoresis GmbH - Carl-Benz-Str.
GEBRAUCHSANLEITUNG Glutatione Agarose Resin Agarose zur Affinitätsreinigung von GST-Tag-Fusionsproteinen und anderen Glutathion-Bindungsproteinen (Kat.-Nr. 42172) SERVA Electrophoresis GmbH - Carl-Benz-Str.
Proteinbestimmung. Diese Lerneinheit befasst sich mit der Beschreibung von verschiedenen Methoden der Proteinbestimmung mit den folgenden Lehrzielen:
 Diese Lerneinheit befasst sich mit der Beschreibung von verschiedenen Methoden der mit den folgenden Lehrzielen: Verständnis der Prinzipien der sowie deren praktischer Durchführung Unterscheidung zwischen
Diese Lerneinheit befasst sich mit der Beschreibung von verschiedenen Methoden der mit den folgenden Lehrzielen: Verständnis der Prinzipien der sowie deren praktischer Durchführung Unterscheidung zwischen
Restriktion zweier Plasmide zur Erstellung einer physikalischen Karte, Grundlagen der DNA- Trennung und Analyse über Agarosegele
 Versuch 1: Restriktionsenzyme als molekulare Werkzeuge Versuchsinhalt Restriktion zweier Plasmide zur Erstellung einer physikalischen Karte, Grundlagen der DNA- Trennung und Analyse über Agarosegele Zwei
Versuch 1: Restriktionsenzyme als molekulare Werkzeuge Versuchsinhalt Restriktion zweier Plasmide zur Erstellung einer physikalischen Karte, Grundlagen der DNA- Trennung und Analyse über Agarosegele Zwei
APP-GFP/Fluoreszenzmikroskop. Aufnahmen neuronaler Zellen, mit freund. Genehmigung von Prof. Stefan Kins, TU Kaiserslautern
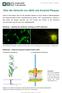 Über die Herkunft von Aβ42 und Amyloid-Plaques Heute ist sicher belegt, dass sich die amyloiden Plaques aus einer Vielzahl an Abbaufragmenten des Amyloid-Vorläufer-Proteins (amyloid-precursor-protein,
Über die Herkunft von Aβ42 und Amyloid-Plaques Heute ist sicher belegt, dass sich die amyloiden Plaques aus einer Vielzahl an Abbaufragmenten des Amyloid-Vorläufer-Proteins (amyloid-precursor-protein,
Versuch 8. Plasmid - Isolierung
 Versuch 8 Plasmid - Isolierung Protokollant: E-mail: Studiengang: Gruppen-Nr: Semester: Betreuer: Max Mustermann [email protected] X X X C. Weindel & M. Schwarz Wird benotet?: Einleitung Ein Plasmid
Versuch 8 Plasmid - Isolierung Protokollant: E-mail: Studiengang: Gruppen-Nr: Semester: Betreuer: Max Mustermann [email protected] X X X C. Weindel & M. Schwarz Wird benotet?: Einleitung Ein Plasmid
Färbung mit AzurGel-K
 Arbeitsanleitung zur Färbung mit AzurGel-K für Gele im Format 10 x 10 x 0,1 cm Kat. Nr.: GF 10002 Ringstr. 4 64401 Gross-Bieberau Tel. ++49-6162-809840 Fax ++49-6162-8098420 www.anamed-gele.com Grundlage
Arbeitsanleitung zur Färbung mit AzurGel-K für Gele im Format 10 x 10 x 0,1 cm Kat. Nr.: GF 10002 Ringstr. 4 64401 Gross-Bieberau Tel. ++49-6162-809840 Fax ++49-6162-8098420 www.anamed-gele.com Grundlage
Protokoll Praktikum für Humanbiologie Studenten
 Protokoll Praktikum für Humanbiologie Studenten Teil A: Charakterisierung der Auswirkungen von γ Interferon auf die Protein und mrna Mengen in humanen A549 Lungenepithelzellen. Studentenaufgaben Tag 1
Protokoll Praktikum für Humanbiologie Studenten Teil A: Charakterisierung der Auswirkungen von γ Interferon auf die Protein und mrna Mengen in humanen A549 Lungenepithelzellen. Studentenaufgaben Tag 1
2.8 Grenzflächeneffekte
 - 86-2.8 Grenzflächeneffekte 2.8.1 Oberflächenspannung An Grenzflächen treten besondere Effekte auf, welche im Volumen nicht beobachtbar sind. Die molekulare Grundlage dafür sind Kohäsionskräfte, d.h.
- 86-2.8 Grenzflächeneffekte 2.8.1 Oberflächenspannung An Grenzflächen treten besondere Effekte auf, welche im Volumen nicht beobachtbar sind. Die molekulare Grundlage dafür sind Kohäsionskräfte, d.h.
Molekulargenetische Experimente IV: Plasmidpräparation
 Molekulargenetische Experimente IV: Plasmidpräparation Plasmide sind kleine, ringförmige DNA-Moleküle in Bakterien, die in der Lage sind, sich selbst mit Hilfe von Enzymen zu replizieren. Gene, die auf
Molekulargenetische Experimente IV: Plasmidpräparation Plasmide sind kleine, ringförmige DNA-Moleküle in Bakterien, die in der Lage sind, sich selbst mit Hilfe von Enzymen zu replizieren. Gene, die auf
Technische Universität Chemnitz Chemisches Grundpraktikum
 Technische Universität Chemnitz Chemisches Grundpraktikum Protokoll «CfP5 - Massanalytische Bestimmungsverfahren (Volumetrie)» Martin Wolf Betreuerin: Frau Sachse Datum:
Technische Universität Chemnitz Chemisches Grundpraktikum Protokoll «CfP5 - Massanalytische Bestimmungsverfahren (Volumetrie)» Martin Wolf Betreuerin: Frau Sachse Datum:
PCD Europe, Krefeld, Jan 2007. Auswertung von Haemoccult
 Auswertung von Haemoccult Ist das positiv? Nein! Ja! Im deutschen Krebsfrüherkennungsprogramm haben nur etwa 1 % der Frauen und 1,5 % der Männer ein positives Haemoccult -Ergebnis, da dieser Test eine
Auswertung von Haemoccult Ist das positiv? Nein! Ja! Im deutschen Krebsfrüherkennungsprogramm haben nur etwa 1 % der Frauen und 1,5 % der Männer ein positives Haemoccult -Ergebnis, da dieser Test eine
Zeichen bei Zahlen entschlüsseln
 Zeichen bei Zahlen entschlüsseln In diesem Kapitel... Verwendung des Zahlenstrahls Absolut richtige Bestimmung von absoluten Werten Operationen bei Zahlen mit Vorzeichen: Addieren, Subtrahieren, Multiplizieren
Zeichen bei Zahlen entschlüsseln In diesem Kapitel... Verwendung des Zahlenstrahls Absolut richtige Bestimmung von absoluten Werten Operationen bei Zahlen mit Vorzeichen: Addieren, Subtrahieren, Multiplizieren
Lineare Funktionen. 1 Proportionale Funktionen 3 1.1 Definition... 3 1.2 Eigenschaften... 3. 2 Steigungsdreieck 3
 Lineare Funktionen Inhaltsverzeichnis 1 Proportionale Funktionen 3 1.1 Definition............................... 3 1.2 Eigenschaften............................. 3 2 Steigungsdreieck 3 3 Lineare Funktionen
Lineare Funktionen Inhaltsverzeichnis 1 Proportionale Funktionen 3 1.1 Definition............................... 3 1.2 Eigenschaften............................. 3 2 Steigungsdreieck 3 3 Lineare Funktionen
50. Mathematik-Olympiade 2. Stufe (Regionalrunde) Klasse 11 13. 501322 Lösung 10 Punkte
 50. Mathematik-Olympiade. Stufe (Regionalrunde) Klasse 3 Lösungen c 00 Aufgabenausschuss des Mathematik-Olympiaden e.v. www.mathematik-olympiaden.de. Alle Rechte vorbehalten. 503 Lösung 0 Punkte Es seien
50. Mathematik-Olympiade. Stufe (Regionalrunde) Klasse 3 Lösungen c 00 Aufgabenausschuss des Mathematik-Olympiaden e.v. www.mathematik-olympiaden.de. Alle Rechte vorbehalten. 503 Lösung 0 Punkte Es seien
Bradford Reagent, 5x
 GEBRAUCHSANLEITUNG Bradford Reagent, 5x Reagenz für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39222) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 HeidelbergPhone +49-6221-138400, Fax +49-6221-1384010
GEBRAUCHSANLEITUNG Bradford Reagent, 5x Reagenz für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39222) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 HeidelbergPhone +49-6221-138400, Fax +49-6221-1384010
Primzahlen und RSA-Verschlüsselung
 Primzahlen und RSA-Verschlüsselung Michael Fütterer und Jonathan Zachhuber 1 Einiges zu Primzahlen Ein paar Definitionen: Wir bezeichnen mit Z die Menge der positiven und negativen ganzen Zahlen, also
Primzahlen und RSA-Verschlüsselung Michael Fütterer und Jonathan Zachhuber 1 Einiges zu Primzahlen Ein paar Definitionen: Wir bezeichnen mit Z die Menge der positiven und negativen ganzen Zahlen, also
Biochemisches Grundpraktikum
 Biochemisches Grundpraktikum Versuch Nummer G-01 01: Potentiometrische und spektrophotometrische Bestim- mung von Ionisationskonstanten Gliederung: I. Titrationskurve von Histidin und Bestimmung der pk-werte...
Biochemisches Grundpraktikum Versuch Nummer G-01 01: Potentiometrische und spektrophotometrische Bestim- mung von Ionisationskonstanten Gliederung: I. Titrationskurve von Histidin und Bestimmung der pk-werte...
Chemie Zusammenfassung KA 2
 Chemie Zusammenfassung KA 2 Wärmemenge Q bei einer Reaktion Chemische Reaktionen haben eine Gemeinsamkeit: Bei der Reaktion wird entweder Energie/Wärme frei (exotherm). Oder es wird Wärme/Energie aufgenommen
Chemie Zusammenfassung KA 2 Wärmemenge Q bei einer Reaktion Chemische Reaktionen haben eine Gemeinsamkeit: Bei der Reaktion wird entweder Energie/Wärme frei (exotherm). Oder es wird Wärme/Energie aufgenommen
Berechnung der Erhöhung der Durchschnittsprämien
 Wolfram Fischer Berechnung der Erhöhung der Durchschnittsprämien Oktober 2004 1 Zusammenfassung Zur Berechnung der Durchschnittsprämien wird das gesamte gemeldete Prämienvolumen Zusammenfassung durch die
Wolfram Fischer Berechnung der Erhöhung der Durchschnittsprämien Oktober 2004 1 Zusammenfassung Zur Berechnung der Durchschnittsprämien wird das gesamte gemeldete Prämienvolumen Zusammenfassung durch die
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr
 Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
SERVA Streptavidin Agarose Resin Agarosematrix zur Affinitätsreinigung von biotinylierten Biomolekülen
 GEBRAUCHSANLEITUNG SERVA Streptavidin Agarose Resin Agarosematrix zur Affinitätsreinigung von biotinylierten Biomolekülen (Kat.-Nr. 42177) SERVA Electrophoresis GmbH - Carl-Benz-Str. 7-69115 Heidelberg
GEBRAUCHSANLEITUNG SERVA Streptavidin Agarose Resin Agarosematrix zur Affinitätsreinigung von biotinylierten Biomolekülen (Kat.-Nr. 42177) SERVA Electrophoresis GmbH - Carl-Benz-Str. 7-69115 Heidelberg
Kapitel 13: Laugen und Neutralisation
 Kapitel 13: Laugen und Neutralisation Alkalimetalle sind Natrium, Kalium, Lithium (und Rubidium, Caesium und Francium). - Welche besonderen Eigenschaften haben die Elemente Natrium, Kalium und Lithium?
Kapitel 13: Laugen und Neutralisation Alkalimetalle sind Natrium, Kalium, Lithium (und Rubidium, Caesium und Francium). - Welche besonderen Eigenschaften haben die Elemente Natrium, Kalium und Lithium?
Erstellen von x-y-diagrammen in OpenOffice.calc
 Erstellen von x-y-diagrammen in OpenOffice.calc In dieser kleinen Anleitung geht es nur darum, aus einer bestehenden Tabelle ein x-y-diagramm zu erzeugen. D.h. es müssen in der Tabelle mindestens zwei
Erstellen von x-y-diagrammen in OpenOffice.calc In dieser kleinen Anleitung geht es nur darum, aus einer bestehenden Tabelle ein x-y-diagramm zu erzeugen. D.h. es müssen in der Tabelle mindestens zwei
Das große ElterngeldPlus 1x1. Alles über das ElterngeldPlus. Wer kann ElterngeldPlus beantragen? ElterngeldPlus verstehen ein paar einleitende Fakten
 Das große x -4 Alles über das Wer kann beantragen? Generell kann jeder beantragen! Eltern (Mütter UND Väter), die schon während ihrer Elternzeit wieder in Teilzeit arbeiten möchten. Eltern, die während
Das große x -4 Alles über das Wer kann beantragen? Generell kann jeder beantragen! Eltern (Mütter UND Väter), die schon während ihrer Elternzeit wieder in Teilzeit arbeiten möchten. Eltern, die während
Lineargleichungssysteme: Additions-/ Subtraktionsverfahren
 Lineargleichungssysteme: Additions-/ Subtraktionsverfahren W. Kippels 22. Februar 2014 Inhaltsverzeichnis 1 Einleitung 2 2 Lineargleichungssysteme zweiten Grades 2 3 Lineargleichungssysteme höheren als
Lineargleichungssysteme: Additions-/ Subtraktionsverfahren W. Kippels 22. Februar 2014 Inhaltsverzeichnis 1 Einleitung 2 2 Lineargleichungssysteme zweiten Grades 2 3 Lineargleichungssysteme höheren als
Übungen zur VL Chemie für Biologen und Humanbiologen 05.12.2011 Lösung Übung 6
 Übungen zur VL Chemie für Biologen und Humanbiologen 05.12.2011 Lösung Übung 6 Thermodynamik und Gleichgewichte 1. a) Was sagt die Enthalpie aus? Die Enthalpie H beschreibt den Energiegehalt von Materie
Übungen zur VL Chemie für Biologen und Humanbiologen 05.12.2011 Lösung Übung 6 Thermodynamik und Gleichgewichte 1. a) Was sagt die Enthalpie aus? Die Enthalpie H beschreibt den Energiegehalt von Materie
Übungsblatt zu Säuren und Basen
 1 Übungsblatt zu Säuren und Basen 1. In einer wässrigen Lösung misst die Konzentration der Oxoniumionen (H 3 O + ) 10 5 M. a) Wie gross ist der ph Wert? b) Ist die Konzentration der OH Ionen grösser oder
1 Übungsblatt zu Säuren und Basen 1. In einer wässrigen Lösung misst die Konzentration der Oxoniumionen (H 3 O + ) 10 5 M. a) Wie gross ist der ph Wert? b) Ist die Konzentration der OH Ionen grösser oder
geben. Die Wahrscheinlichkeit von 100% ist hier demnach nur der Gehen wir einmal davon aus, dass die von uns angenommenen
 geben. Die Wahrscheinlichkeit von 100% ist hier demnach nur der Vollständigkeit halber aufgeführt. Gehen wir einmal davon aus, dass die von uns angenommenen 70% im Beispiel exakt berechnet sind. Was würde
geben. Die Wahrscheinlichkeit von 100% ist hier demnach nur der Vollständigkeit halber aufgeführt. Gehen wir einmal davon aus, dass die von uns angenommenen 70% im Beispiel exakt berechnet sind. Was würde
Ein süsses Experiment
 Ein süsses Experiment Zuckerkristalle am Stiel Das brauchst du: 250 Milliliter Wasser (entspricht etwa einer Tasse). Das reicht für 4-5 kleine Marmeladengläser und 4-5 Zuckerstäbchen 650 Gramm Zucker (den
Ein süsses Experiment Zuckerkristalle am Stiel Das brauchst du: 250 Milliliter Wasser (entspricht etwa einer Tasse). Das reicht für 4-5 kleine Marmeladengläser und 4-5 Zuckerstäbchen 650 Gramm Zucker (den
Wie Sie mit Mastern arbeiten
 Wie Sie mit Mastern arbeiten Was ist ein Master? Einer der großen Vorteile von EDV besteht darin, dass Ihnen der Rechner Arbeit abnimmt. Diesen Vorteil sollten sie nutzen, wo immer es geht. In PowerPoint
Wie Sie mit Mastern arbeiten Was ist ein Master? Einer der großen Vorteile von EDV besteht darin, dass Ihnen der Rechner Arbeit abnimmt. Diesen Vorteil sollten sie nutzen, wo immer es geht. In PowerPoint
Säure-Base Titrationen. (Seminar zu den Übungen zur quantitativen Bestimmung von Arznei-, Hilfs- und Schadstoffen)
 Säure-Base Titrationen (Seminar zu den Übungen zur quantitativen Bestimmung von Arznei-, Hilfs- und Schadstoffen) 1. Gehaltsbestimmung von Salzsäure HCl ist eine starke Säure (fast zu 100% dissoziiert)
Säure-Base Titrationen (Seminar zu den Übungen zur quantitativen Bestimmung von Arznei-, Hilfs- und Schadstoffen) 1. Gehaltsbestimmung von Salzsäure HCl ist eine starke Säure (fast zu 100% dissoziiert)
Johannes Gutenberg-Universität Mainz Fachbereich Biologie, Institut für Zoologie Leitung: Prof. Dr. Wolfrum Datum: 15. April 2005
 Johannes Gutenberg-Universität Mainz Fachbereich Biologie, Institut für Zoologie Leitung: Prof. Dr. Wolfrum Datum: 15. April 2005 F1 Molekulare Zoologie Teil II: Expressionsanalyse Proteinexpressionsanalyse
Johannes Gutenberg-Universität Mainz Fachbereich Biologie, Institut für Zoologie Leitung: Prof. Dr. Wolfrum Datum: 15. April 2005 F1 Molekulare Zoologie Teil II: Expressionsanalyse Proteinexpressionsanalyse
SingleQuant Assay Kit
 GEBRAUCHSANLEITUNG SingleQuant Assay Kit Kit für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39226) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010
GEBRAUCHSANLEITUNG SingleQuant Assay Kit Kit für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39226) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010
Datensicherung. Beschreibung der Datensicherung
 Datensicherung Mit dem Datensicherungsprogramm können Sie Ihre persönlichen Daten problemlos Sichern. Es ist möglich eine komplette Datensicherung durchzuführen, aber auch nur die neuen und geänderten
Datensicherung Mit dem Datensicherungsprogramm können Sie Ihre persönlichen Daten problemlos Sichern. Es ist möglich eine komplette Datensicherung durchzuführen, aber auch nur die neuen und geänderten
Stationsunterricht im Physikunterricht der Klasse 10
 Oranke-Oberschule Berlin (Gymnasium) Konrad-Wolf-Straße 11 13055 Berlin Frau Dr. D. Meyerhöfer Stationsunterricht im Physikunterricht der Klasse 10 Experimente zur spezifischen Wärmekapazität von Körpern
Oranke-Oberschule Berlin (Gymnasium) Konrad-Wolf-Straße 11 13055 Berlin Frau Dr. D. Meyerhöfer Stationsunterricht im Physikunterricht der Klasse 10 Experimente zur spezifischen Wärmekapazität von Körpern
Anleitung zur Daten zur Datensicherung und Datenrücksicherung. Datensicherung
 Anleitung zur Daten zur Datensicherung und Datenrücksicherung Datensicherung Es gibt drei Möglichkeiten der Datensicherung. Zwei davon sind in Ges eingebaut, die dritte ist eine manuelle Möglichkeit. In
Anleitung zur Daten zur Datensicherung und Datenrücksicherung Datensicherung Es gibt drei Möglichkeiten der Datensicherung. Zwei davon sind in Ges eingebaut, die dritte ist eine manuelle Möglichkeit. In
1 topologisches Sortieren
 Wolfgang Hönig / Andreas Ecke WS 09/0 topologisches Sortieren. Überblick. Solange noch Knoten vorhanden: a) Suche Knoten v, zu dem keine Kante führt (Falls nicht vorhanden keine topologische Sortierung
Wolfgang Hönig / Andreas Ecke WS 09/0 topologisches Sortieren. Überblick. Solange noch Knoten vorhanden: a) Suche Knoten v, zu dem keine Kante führt (Falls nicht vorhanden keine topologische Sortierung
Versuch: Siedediagramm eines binären Gemisches
 Versuch: Siedediagramm eines binären Gemisches Aufgaben - Kalibriermessungen Bestimmen Sie experimentell den Brechungsindex einer gegebenen Mischung bei unterschiedlicher Zusammensetzung. - Theoretische
Versuch: Siedediagramm eines binären Gemisches Aufgaben - Kalibriermessungen Bestimmen Sie experimentell den Brechungsindex einer gegebenen Mischung bei unterschiedlicher Zusammensetzung. - Theoretische
4.1. Herstellung des CH2/CH3-trunkierten dimerisierten anti-cd30-igg1-tnf- Fusionsproteins
 ERGEBNISSE 29 4. Ergebnisse 4.1. Herstellung des CH2/CH3-trunkierten dimerisierten anti-cd3-igg1-tnf- Fusionsproteins Im vorliegenden Immunzytokin wurden die Domänen CH2/CH3 des humanen Fc-Fragmentes durch
ERGEBNISSE 29 4. Ergebnisse 4.1. Herstellung des CH2/CH3-trunkierten dimerisierten anti-cd3-igg1-tnf- Fusionsproteins Im vorliegenden Immunzytokin wurden die Domänen CH2/CH3 des humanen Fc-Fragmentes durch
Auf der Suche nach der Wundermedizin
 Auf der Suche nach der Wundermedizin Experimente im Schullabor 1 Herausgeber Novartis Pharma AG, CH-4002 Basel Autoren: Dr. Gesche Standke und Dr. Christiane Röckl Michel Zeichnungen: Fonds der Chemischen
Auf der Suche nach der Wundermedizin Experimente im Schullabor 1 Herausgeber Novartis Pharma AG, CH-4002 Basel Autoren: Dr. Gesche Standke und Dr. Christiane Röckl Michel Zeichnungen: Fonds der Chemischen
OECD Programme for International Student Assessment PISA 2000. Lösungen der Beispielaufgaben aus dem Mathematiktest. Deutschland
 OECD Programme for International Student Assessment Deutschland PISA 2000 Lösungen der Beispielaufgaben aus dem Mathematiktest Beispielaufgaben PISA-Hauptstudie 2000 Seite 3 UNIT ÄPFEL Beispielaufgaben
OECD Programme for International Student Assessment Deutschland PISA 2000 Lösungen der Beispielaufgaben aus dem Mathematiktest Beispielaufgaben PISA-Hauptstudie 2000 Seite 3 UNIT ÄPFEL Beispielaufgaben
Professionelle Seminare im Bereich MS-Office
 Der Name BEREICH.VERSCHIEBEN() ist etwas unglücklich gewählt. Man kann mit der Funktion Bereiche zwar verschieben, man kann Bereiche aber auch verkleinern oder vergrößern. Besser wäre es, die Funktion
Der Name BEREICH.VERSCHIEBEN() ist etwas unglücklich gewählt. Man kann mit der Funktion Bereiche zwar verschieben, man kann Bereiche aber auch verkleinern oder vergrößern. Besser wäre es, die Funktion
Einführung in die Algebra
 Prof. Dr. H. Brenner Osnabrück SS 2009 Einführung in die Algebra Vorlesung 13 Einheiten Definition 13.1. Ein Element u in einem Ring R heißt Einheit, wenn es ein Element v R gibt mit uv = vu = 1. DasElementv
Prof. Dr. H. Brenner Osnabrück SS 2009 Einführung in die Algebra Vorlesung 13 Einheiten Definition 13.1. Ein Element u in einem Ring R heißt Einheit, wenn es ein Element v R gibt mit uv = vu = 1. DasElementv
Titration einer Säure mit einer Base
 Titration einer Säure mit einer Base Peter Bützer Inhalt 1 Einleitung... 1 2 Modellannahmen (Systemdynamik)... 2 3 Simulationsdiagramm (Typ 1)... 2 4 Dokumentation (Gleichungen, Parameter)... 3 5 Simulation...
Titration einer Säure mit einer Base Peter Bützer Inhalt 1 Einleitung... 1 2 Modellannahmen (Systemdynamik)... 2 3 Simulationsdiagramm (Typ 1)... 2 4 Dokumentation (Gleichungen, Parameter)... 3 5 Simulation...
Die Größe von Flächen vergleichen
 Vertiefen 1 Die Größe von Flächen vergleichen zu Aufgabe 1 Schulbuch, Seite 182 1 Wer hat am meisten Platz? Ordne die Figuren nach ihrem Flächeninhalt. Begründe deine Reihenfolge. 1 2 3 4 zu Aufgabe 2
Vertiefen 1 Die Größe von Flächen vergleichen zu Aufgabe 1 Schulbuch, Seite 182 1 Wer hat am meisten Platz? Ordne die Figuren nach ihrem Flächeninhalt. Begründe deine Reihenfolge. 1 2 3 4 zu Aufgabe 2
Lineare Gleichungssysteme
 Lineare Gleichungssysteme 1 Zwei Gleichungen mit zwei Unbekannten Es kommt häufig vor, dass man nicht mit einer Variablen alleine auskommt, um ein Problem zu lösen. Das folgende Beispiel soll dies verdeutlichen
Lineare Gleichungssysteme 1 Zwei Gleichungen mit zwei Unbekannten Es kommt häufig vor, dass man nicht mit einer Variablen alleine auskommt, um ein Problem zu lösen. Das folgende Beispiel soll dies verdeutlichen
RIAG Zn 230. Cyanidisches Glanzzinkverfahren
 Postfach 169 CH-9545 Wängi TG 20.08.2009 RIAG Zn 230 Cyanidisches Glanzzinkverfahren Eigenschaften Das cyanidische Glanzzinkverfahren RIAG Zn 230 erzeugt glänzende Niederschläge über einen weiten Stromdichtebereich.
Postfach 169 CH-9545 Wängi TG 20.08.2009 RIAG Zn 230 Cyanidisches Glanzzinkverfahren Eigenschaften Das cyanidische Glanzzinkverfahren RIAG Zn 230 erzeugt glänzende Niederschläge über einen weiten Stromdichtebereich.
Unterrichtsmaterialien in digitaler und in gedruckter Form. Auszug aus: Übungsbuch für den Grundkurs mit Tipps und Lösungen: Analysis
 Unterrichtsmaterialien in digitaler und in gedruckter Form Auszug aus: Übungsbuch für den Grundkurs mit Tipps und Lösungen: Analysis Das komplette Material finden Sie hier: Download bei School-Scout.de
Unterrichtsmaterialien in digitaler und in gedruckter Form Auszug aus: Übungsbuch für den Grundkurs mit Tipps und Lösungen: Analysis Das komplette Material finden Sie hier: Download bei School-Scout.de
Plasmidpräparation aus Bakterien Inhalt
 Inhalt Einleitung... 2 Materialien... 4 Gewinnung der Bakterien... 6 Zerstörung der Bakterien... 7 Trennung von Plasmid-DNA und genomischer DNA... 8 Reinigung der Plasmid-DNA... 10 Elution der gereinigten
Inhalt Einleitung... 2 Materialien... 4 Gewinnung der Bakterien... 6 Zerstörung der Bakterien... 7 Trennung von Plasmid-DNA und genomischer DNA... 8 Reinigung der Plasmid-DNA... 10 Elution der gereinigten
Musterprüfung Chemie Klassen: MPL 09 Datum: 14. 16. April 2010
 1 Musterprüfung Chemie Klassen: MPL 09 Datum: 14. 16. April 2010 Themen: Metallische Bindungen (Skript S. 51 53, inkl. Arbeitsblatt) Reaktionsverlauf (Skript S. 54 59, inkl. Arbeitsblatt, Merke, Fig. 7.2.1
1 Musterprüfung Chemie Klassen: MPL 09 Datum: 14. 16. April 2010 Themen: Metallische Bindungen (Skript S. 51 53, inkl. Arbeitsblatt) Reaktionsverlauf (Skript S. 54 59, inkl. Arbeitsblatt, Merke, Fig. 7.2.1
GEVITAS Farben-Reaktionstest
 GEVITAS Farben-Reaktionstest GEVITAS Farben-Reaktionstest Inhalt 1. Allgemeines... 1 2. Funktionsweise der Tests... 2 3. Die Ruhetaste und die Auslösetaste... 2 4. Starten der App Hauptmenü... 3 5. Auswahl
GEVITAS Farben-Reaktionstest GEVITAS Farben-Reaktionstest Inhalt 1. Allgemeines... 1 2. Funktionsweise der Tests... 2 3. Die Ruhetaste und die Auslösetaste... 2 4. Starten der App Hauptmenü... 3 5. Auswahl
Praktikum: Nachweis einer gentechnischen Veränderung in Lebensmitteln durch PCR
 Praktikum: Nachweis einer gentechnischen Veränderung in Lebensmitteln durch PCR Vorbereitung Lehrer Für jede Arbeitsgruppe werden 550 µl InstaGene-Matrix aliquotiert! Das Tube wird mit IG beschriftet!
Praktikum: Nachweis einer gentechnischen Veränderung in Lebensmitteln durch PCR Vorbereitung Lehrer Für jede Arbeitsgruppe werden 550 µl InstaGene-Matrix aliquotiert! Das Tube wird mit IG beschriftet!
Repetitionsaufgaben Wurzelgleichungen
 Repetitionsaufgaben Wurzelgleichungen Inhaltsverzeichnis A) Vorbemerkungen B) Lernziele C) Theorie mit Aufgaben D) Aufgaben mit Musterlösungen 4 A) Vorbemerkungen Bitte beachten Sie: Bei Wurzelgleichungen
Repetitionsaufgaben Wurzelgleichungen Inhaltsverzeichnis A) Vorbemerkungen B) Lernziele C) Theorie mit Aufgaben D) Aufgaben mit Musterlösungen 4 A) Vorbemerkungen Bitte beachten Sie: Bei Wurzelgleichungen
Selbst-Test zur Vorab-Einschätzung zum Vorkurs Chemie für Mediziner
 Liebe Studierende der Human- und Zahnmedizin, mithilfe dieses Tests können Sie selbst einschätzen, ob Sie den Vorkurs besuchen sollten. Die kleine Auswahl an Aufgaben spiegelt in etwa das Niveau des Vorkurses
Liebe Studierende der Human- und Zahnmedizin, mithilfe dieses Tests können Sie selbst einschätzen, ob Sie den Vorkurs besuchen sollten. Die kleine Auswahl an Aufgaben spiegelt in etwa das Niveau des Vorkurses
Fotos in Tobii Communicator verwenden
 Fotos in Tobii Communicator verwenden Hier wird beschrieben wie man Fotos in Tobii Communicator verwenden kann und was man zur Nutzung beachten sollte. Fotonutzung in Tobii Communicator In einigen Fällen
Fotos in Tobii Communicator verwenden Hier wird beschrieben wie man Fotos in Tobii Communicator verwenden kann und was man zur Nutzung beachten sollte. Fotonutzung in Tobii Communicator In einigen Fällen
V 2 B, C, D Drinks. Möglicher Lösungsweg a) Gleichungssystem: 300x + 400 y = 520 300x + 500y = 597,5 2x3 Matrix: Energydrink 0,7 Mineralwasser 0,775,
 Aufgabenpool für angewandte Mathematik / 1. Jahrgang V B, C, D Drinks Ein gastronomischer Betrieb kauft 300 Dosen Energydrinks (0,3 l) und 400 Liter Flaschen Mineralwasser und zahlt dafür 50, Euro. Einen
Aufgabenpool für angewandte Mathematik / 1. Jahrgang V B, C, D Drinks Ein gastronomischer Betrieb kauft 300 Dosen Energydrinks (0,3 l) und 400 Liter Flaschen Mineralwasser und zahlt dafür 50, Euro. Einen
Das RSA-Verschlüsselungsverfahren 1 Christian Vollmer
 Das RSA-Verschlüsselungsverfahren 1 Christian Vollmer Allgemein: Das RSA-Verschlüsselungsverfahren ist ein häufig benutztes Verschlüsselungsverfahren, weil es sehr sicher ist. Es gehört zu der Klasse der
Das RSA-Verschlüsselungsverfahren 1 Christian Vollmer Allgemein: Das RSA-Verschlüsselungsverfahren ist ein häufig benutztes Verschlüsselungsverfahren, weil es sehr sicher ist. Es gehört zu der Klasse der
Einen Wiederherstellungspunktes erstellen & Rechner mit Hilfe eines Wiederherstellungspunktes zu einem früheren Zeitpunkt wieder herstellen
 Einen Wiederherstellungspunktes erstellen & Rechner mit Hilfe eines Wiederherstellungspunktes zu einem früheren Zeitpunkt wieder herstellen 1 Hier einige Links zu Dokumentationen im WEB Windows XP: http://www.verbraucher-sicher-online.de/node/18
Einen Wiederherstellungspunktes erstellen & Rechner mit Hilfe eines Wiederherstellungspunktes zu einem früheren Zeitpunkt wieder herstellen 1 Hier einige Links zu Dokumentationen im WEB Windows XP: http://www.verbraucher-sicher-online.de/node/18
file://c:\documents and Settings\kfzhans.BUERO1\Local Settings\Temp\39801700-e...
 Page 1 of 5 Komponentennummer 31 Identifikation Die Funktionsweise dieser Sensoren ist normalerweise überall gleich, obwohl sie sich je nach Anwendung oder Hersteller in der Konstruktion unterscheiden
Page 1 of 5 Komponentennummer 31 Identifikation Die Funktionsweise dieser Sensoren ist normalerweise überall gleich, obwohl sie sich je nach Anwendung oder Hersteller in der Konstruktion unterscheiden
aktualisiert, 10.03.2011, Wera Roth, DE1 WESTERN BLOT
 1 aktualisiert, 10.03.2011, Wera Roth, DE1 WESTERN BLOT 1. Hinweise zu Membranen a. Nitrocellulose b. PVDF (alternativ) 2. Aufbau des Transfers a. Naßblot b. Semi-dry (alternativ) 3. Färben und Dokumentation
1 aktualisiert, 10.03.2011, Wera Roth, DE1 WESTERN BLOT 1. Hinweise zu Membranen a. Nitrocellulose b. PVDF (alternativ) 2. Aufbau des Transfers a. Naßblot b. Semi-dry (alternativ) 3. Färben und Dokumentation
6 Schulungsmodul: Probenahme im Betrieb
 6 Schulungsmodul: Probenahme im Betrieb WIEDNER Wie schon im Kapitel VI erwähnt, ist die Probenahme in Betrieben, die Produkte nach dem Lebensmittel- und Futtermittelgesetzbuch herstellen oder in den Verkehr
6 Schulungsmodul: Probenahme im Betrieb WIEDNER Wie schon im Kapitel VI erwähnt, ist die Probenahme in Betrieben, die Produkte nach dem Lebensmittel- und Futtermittelgesetzbuch herstellen oder in den Verkehr
8.2 Thermodynamische Gleichgewichte, insbesondere Gleichgewichte in Mehrkomponentensystemen Mechanisches und thermisches Gleichgewicht
 8.2 Thermodynamische Gleichgewichte, insbesondere Gleichgewichte in Mehrkomponentensystemen Mechanisches und thermisches Gleichgewicht 8.2-1 Stoffliches Gleichgewicht Beispiel Stickstoff Sauerstoff: Desweiteren
8.2 Thermodynamische Gleichgewichte, insbesondere Gleichgewichte in Mehrkomponentensystemen Mechanisches und thermisches Gleichgewicht 8.2-1 Stoffliches Gleichgewicht Beispiel Stickstoff Sauerstoff: Desweiteren
Trennungsverfahren Techniken (in der Biologie)
 Trennungsverfahren Techniken (in der Biologie)? Biomoleküle können getrennt werden aufgrund ihrer - chemischen Eigenschaften: Ladung, Löslichkeit, Wechselwirkung mit spezifischen Reagenzen, Molmasse -
Trennungsverfahren Techniken (in der Biologie)? Biomoleküle können getrennt werden aufgrund ihrer - chemischen Eigenschaften: Ladung, Löslichkeit, Wechselwirkung mit spezifischen Reagenzen, Molmasse -
7. Bewässerung: Mehrmals pro Woche
 7. Bewässerung: Mehrmals pro Woche Eine Kultur im Erdboden muss mehrmals wöchentlich bewässert werden. 1. Erstellen Sie ein Arbeitsblatt 2. Pumpe 3. Ventilgruppe 1 4. Kulturfachregelung 5. Wasser-Anschlüsse
7. Bewässerung: Mehrmals pro Woche Eine Kultur im Erdboden muss mehrmals wöchentlich bewässert werden. 1. Erstellen Sie ein Arbeitsblatt 2. Pumpe 3. Ventilgruppe 1 4. Kulturfachregelung 5. Wasser-Anschlüsse
Protokoll 2. Labor für Physikalische Chemie. Modul IV. Säure-Base-Reaktion. Versuch 5.1 5.2. Neutralisation, Gehaltsbestimmungen und Titrationskurven
 Protokoll 2 Labor für Physikalische Chemie Modul IV Säure-Base-Reaktion Versuch 5.1 5.2 Neutralisation, Gehaltsbestimmungen und Titrationskurven Fachbereich MT 1 Wintersemester 2005/2006 Thorsten Huber,
Protokoll 2 Labor für Physikalische Chemie Modul IV Säure-Base-Reaktion Versuch 5.1 5.2 Neutralisation, Gehaltsbestimmungen und Titrationskurven Fachbereich MT 1 Wintersemester 2005/2006 Thorsten Huber,
Titration. Weiterbildung für fachfremd unterrichtende Lehrkräfte
 Titration Weiterbildung für fachfremd unterrichtende Lehrkräfte Chromatografi e von Blattfarbstoffen Destillation von Rotwein Zerlegung der Verbindung Wasser Herstellung von Natronlauge Öltröpfchen versuch
Titration Weiterbildung für fachfremd unterrichtende Lehrkräfte Chromatografi e von Blattfarbstoffen Destillation von Rotwein Zerlegung der Verbindung Wasser Herstellung von Natronlauge Öltröpfchen versuch
1. Man schreibe die folgenden Aussagen jeweils in einen normalen Satz um. Zum Beispiel kann man die Aussage:
 Zählen und Zahlbereiche Übungsblatt 1 1. Man schreibe die folgenden Aussagen jeweils in einen normalen Satz um. Zum Beispiel kann man die Aussage: Für alle m, n N gilt m + n = n + m. in den Satz umschreiben:
Zählen und Zahlbereiche Übungsblatt 1 1. Man schreibe die folgenden Aussagen jeweils in einen normalen Satz um. Zum Beispiel kann man die Aussage: Für alle m, n N gilt m + n = n + m. in den Satz umschreiben:
Info zum Zusammenhang von Auflösung und Genauigkeit
 Da es oft Nachfragen und Verständnisprobleme mit den oben genannten Begriffen gibt, möchten wir hier versuchen etwas Licht ins Dunkel zu bringen. Nehmen wir mal an, Sie haben ein Stück Wasserrohr mit der
Da es oft Nachfragen und Verständnisprobleme mit den oben genannten Begriffen gibt, möchten wir hier versuchen etwas Licht ins Dunkel zu bringen. Nehmen wir mal an, Sie haben ein Stück Wasserrohr mit der
Übung 5 : G = Wärmeflussdichte [Watt/m 2 ] c = spezifische Wärmekapazität k = Wärmeleitfähigkeit = *p*c = Wärmediffusität
![Übung 5 : G = Wärmeflussdichte [Watt/m 2 ] c = spezifische Wärmekapazität k = Wärmeleitfähigkeit = *p*c = Wärmediffusität Übung 5 : G = Wärmeflussdichte [Watt/m 2 ] c = spezifische Wärmekapazität k = Wärmeleitfähigkeit = *p*c = Wärmediffusität](/thumbs/26/9283097.jpg) Übung 5 : Theorie : In einem Boden finden immer Temperaturausgleichsprozesse statt. Der Wärmestrom läßt sich in eine vertikale und horizontale Komponente einteilen. Wir betrachten hier den Wärmestrom in
Übung 5 : Theorie : In einem Boden finden immer Temperaturausgleichsprozesse statt. Der Wärmestrom läßt sich in eine vertikale und horizontale Komponente einteilen. Wir betrachten hier den Wärmestrom in
2 Physikalische Eigenschaften von Fettsäuren: Löslichkeit, Dissoziationsverhalten, Phasenzustände
 2 Physikalische Eigenschaften von Fettsäuren: Löslichkeit, Dissoziationsverhalten, Phasenzustände Als Fettsäuren wird die Gruppe aliphatischer Monocarbonsäuren bezeichnet. Der Name Fettsäuren geht darauf
2 Physikalische Eigenschaften von Fettsäuren: Löslichkeit, Dissoziationsverhalten, Phasenzustände Als Fettsäuren wird die Gruppe aliphatischer Monocarbonsäuren bezeichnet. Der Name Fettsäuren geht darauf
Probe und Probenmenge Wassermenge Auftragspuffermenge 5 µl Kaninchenmuskelextrakt 50 µl 100 µl
 Arbeitsgruppe D 6 Clara Dees Susanne Duncker Anja Hartmann Kristin Hofmann Kurs 3: Proteinanalysen Im heutigen Kurs extrahierten wir zum einen Proteine aus verschiedenen Geweben eines Kaninchens und führten
Arbeitsgruppe D 6 Clara Dees Susanne Duncker Anja Hartmann Kristin Hofmann Kurs 3: Proteinanalysen Im heutigen Kurs extrahierten wir zum einen Proteine aus verschiedenen Geweben eines Kaninchens und führten
ERGÄNZUNGEN ZUR ANALYSIS II MITTELWERTSATZ UND ANWENDUNGEN
 ERGÄNZUNGEN ZUR ANALYSIS II MITTELWERTSATZ UND ANWENDUNGEN CHRISTIAN HARTFELDT. Zweiter Mittelwertsatz Der Mittelwertsatz Satz VI.3.4) lässt sich verallgemeinern zu Satz.. Seien f, g : [a, b] R auf [a,
ERGÄNZUNGEN ZUR ANALYSIS II MITTELWERTSATZ UND ANWENDUNGEN CHRISTIAN HARTFELDT. Zweiter Mittelwertsatz Der Mittelwertsatz Satz VI.3.4) lässt sich verallgemeinern zu Satz.. Seien f, g : [a, b] R auf [a,
Durchführung einer Gel-Elektrophorese mit einem DNA-Gemisch
 Durchführung einer Gel-Elektrophorese mit einem DNA-Gemisch (Fotos vom 6. März 2013 Molekularbiologisches Praktikum 12 G-Kurs Biologie Herr Korne - am KOMM Homburg/Saar unter Anleitung von Frau Dr. Amoroso)
Durchführung einer Gel-Elektrophorese mit einem DNA-Gemisch (Fotos vom 6. März 2013 Molekularbiologisches Praktikum 12 G-Kurs Biologie Herr Korne - am KOMM Homburg/Saar unter Anleitung von Frau Dr. Amoroso)
Anleitung über den Umgang mit Schildern
 Anleitung über den Umgang mit Schildern -Vorwort -Wo bekommt man Schilder? -Wo und wie speichert man die Schilder? -Wie füge ich die Schilder in meinen Track ein? -Welche Bauteile kann man noch für Schilder
Anleitung über den Umgang mit Schildern -Vorwort -Wo bekommt man Schilder? -Wo und wie speichert man die Schilder? -Wie füge ich die Schilder in meinen Track ein? -Welche Bauteile kann man noch für Schilder
Download. Mathematik üben Klasse 8 Funktionen. Differenzierte Materialien für das ganze Schuljahr. Jens Conrad, Hardy Seifert
 Download Jens Conrad, Hard Seifert Mathematik üben Klasse 8 Funktionen Differenzierte Materialien für das ganze Schuljahr Downloadauszug aus dem Originaltitel: Mathematik üben Klasse 8 Funktionen Differenzierte
Download Jens Conrad, Hard Seifert Mathematik üben Klasse 8 Funktionen Differenzierte Materialien für das ganze Schuljahr Downloadauszug aus dem Originaltitel: Mathematik üben Klasse 8 Funktionen Differenzierte
6.2 Scan-Konvertierung (Scan Conversion)
 6.2 Scan-Konvertierung (Scan Conversion) Scan-Konvertierung ist die Rasterung von einfachen Objekten (Geraden, Kreisen, Kurven). Als Ausgabemedium dient meist der Bildschirm, der aus einem Pixelraster
6.2 Scan-Konvertierung (Scan Conversion) Scan-Konvertierung ist die Rasterung von einfachen Objekten (Geraden, Kreisen, Kurven). Als Ausgabemedium dient meist der Bildschirm, der aus einem Pixelraster
Rund ums Fahrrad Ein Unterrichtsprojekt für den 7. Jahrgang
 Fahrrad Sicherheit: Jedes Fahrrad muss verkehrssicher sein, sonst darf es nicht am Straßenverkehr teilnehmen. Die meisten benutzten Fahrräder erfüllen die Kriterien der Verkehrssicherheit nicht. Beschreibe
Fahrrad Sicherheit: Jedes Fahrrad muss verkehrssicher sein, sonst darf es nicht am Straßenverkehr teilnehmen. Die meisten benutzten Fahrräder erfüllen die Kriterien der Verkehrssicherheit nicht. Beschreibe
Plasmid DNA purification
 Plasmid DNA purification Excerpt from user manual - Deutsch - NucleoBond Xtra NucleoBond Xtra NucleoBond Xtra Plus NucleoBond Xtra Plus January 2013 / Rev. 11 Plasmid DNA Purification Deutsch Einleitung
Plasmid DNA purification Excerpt from user manual - Deutsch - NucleoBond Xtra NucleoBond Xtra NucleoBond Xtra Plus NucleoBond Xtra Plus January 2013 / Rev. 11 Plasmid DNA Purification Deutsch Einleitung
Praktikum Biochemie Einführung in die Molekularbiologie. Bettina Siebers
 Praktikum Biochemie Einführung in die Molekularbiologie Bettina Siebers (4) Rekombinante Expression einer Esterase aus Pseudomonas aeruginosa in E. coli Proteinreinigung Techniken & Methoden der Proteinreinigung
Praktikum Biochemie Einführung in die Molekularbiologie Bettina Siebers (4) Rekombinante Expression einer Esterase aus Pseudomonas aeruginosa in E. coli Proteinreinigung Techniken & Methoden der Proteinreinigung
Erstellen einer Collage. Zuerst ein leeres Dokument erzeugen, auf dem alle anderen Bilder zusammengefügt werden sollen (über [Datei] > [Neu])
![Erstellen einer Collage. Zuerst ein leeres Dokument erzeugen, auf dem alle anderen Bilder zusammengefügt werden sollen (über [Datei] > [Neu]) Erstellen einer Collage. Zuerst ein leeres Dokument erzeugen, auf dem alle anderen Bilder zusammengefügt werden sollen (über [Datei] > [Neu])](/thumbs/29/13170670.jpg) 3.7 Erstellen einer Collage Zuerst ein leeres Dokument erzeugen, auf dem alle anderen Bilder zusammengefügt werden sollen (über [Datei] > [Neu]) Dann Größe des Dokuments festlegen beispielsweise A4 (weitere
3.7 Erstellen einer Collage Zuerst ein leeres Dokument erzeugen, auf dem alle anderen Bilder zusammengefügt werden sollen (über [Datei] > [Neu]) Dann Größe des Dokuments festlegen beispielsweise A4 (weitere
Kapitalerhöhung - Verbuchung
 Kapitalerhöhung - Verbuchung Beschreibung Eine Kapitalerhöhung ist eine Erhöhung des Aktienkapitals einer Aktiengesellschaft durch Emission von en Aktien. Es gibt unterschiedliche Formen von Kapitalerhöhung.
Kapitalerhöhung - Verbuchung Beschreibung Eine Kapitalerhöhung ist eine Erhöhung des Aktienkapitals einer Aktiengesellschaft durch Emission von en Aktien. Es gibt unterschiedliche Formen von Kapitalerhöhung.
WLAN und VPN im b.i.b. mit Windows (Vista Home Premium SP1) oder Windows 7
 WLAN Bei Windows Vista Home Premium mit Service Pack 1 wrd unten rechts im Tray angezeigt, wenn Drahtlosnetzwerke verfügbar sind, ebenso bei Windows 7. Solange keine Verbindung mit diesen Drahtlosnetzwerken
WLAN Bei Windows Vista Home Premium mit Service Pack 1 wrd unten rechts im Tray angezeigt, wenn Drahtlosnetzwerke verfügbar sind, ebenso bei Windows 7. Solange keine Verbindung mit diesen Drahtlosnetzwerken
Nach der Anmeldung im Backend Bereich landen Sie im Kontrollzentrum, welches so aussieht:
 Beiträge erstellen in Joomla Nach der Anmeldung im Backend Bereich landen Sie im Kontrollzentrum, welches so aussieht: Abbildung 1 - Kontrollzentrum Von hier aus kann man zu verschiedene Einstellungen
Beiträge erstellen in Joomla Nach der Anmeldung im Backend Bereich landen Sie im Kontrollzentrum, welches so aussieht: Abbildung 1 - Kontrollzentrum Von hier aus kann man zu verschiedene Einstellungen
Mind Mapping am PC. für Präsentationen, Vorträge, Selbstmanagement. von Isolde Kommer, Helmut Reinke. 1. Auflage. Hanser München 1999
 Mind Mapping am PC für Präsentationen, Vorträge, Selbstmanagement von Isolde Kommer, Helmut Reinke 1. Auflage Hanser München 1999 Verlag C.H. Beck im Internet: www.beck.de ISBN 978 3 446 21222 0 schnell
Mind Mapping am PC für Präsentationen, Vorträge, Selbstmanagement von Isolde Kommer, Helmut Reinke 1. Auflage Hanser München 1999 Verlag C.H. Beck im Internet: www.beck.de ISBN 978 3 446 21222 0 schnell
Inhalt. 1. Einleitung Seite 3. 2. Schritt für Schritt Seite 4. 3. Tipps und Tricks Seite 6
 Gebrauchsanleitung Inhalt 1. Einleitung Seite 3 2. Schritt für Schritt Seite 4 3. Tipps und Tricks Seite 6 2 Einleitung Vielen Dank, dass Sie einer GrooVi-Maschine den Vorzug gegeben haben! Diese Gebrauchsanleitung
Gebrauchsanleitung Inhalt 1. Einleitung Seite 3 2. Schritt für Schritt Seite 4 3. Tipps und Tricks Seite 6 2 Einleitung Vielen Dank, dass Sie einer GrooVi-Maschine den Vorzug gegeben haben! Diese Gebrauchsanleitung
HOWTO Update von MRG1 auf MRG2 bei gleichzeitigem Update auf Magento CE 1.4 / Magento EE 1.8
 Update von MRG1 auf MRG2 bei gleichzeitigem Update auf Magento CE 1.4 / Magento EE 1.8 Schritt 1: Altes Modul-Paket vollständig deinstallieren Die neuen MRG-Module sind aus dem Scope local in den Scope
Update von MRG1 auf MRG2 bei gleichzeitigem Update auf Magento CE 1.4 / Magento EE 1.8 Schritt 1: Altes Modul-Paket vollständig deinstallieren Die neuen MRG-Module sind aus dem Scope local in den Scope
Im Jahr t = 0 hat eine Stadt 10.000 Einwohner. Nach 15 Jahren hat sich die Einwohnerzahl verdoppelt. z(t) = at + b
 Aufgabe 1: Im Jahr t = 0 hat eine Stadt 10.000 Einwohner. Nach 15 Jahren hat sich die Einwohnerzahl verdoppelt. (a) Nehmen Sie lineares Wachstum gemäß z(t) = at + b an, wobei z die Einwohnerzahl ist und
Aufgabe 1: Im Jahr t = 0 hat eine Stadt 10.000 Einwohner. Nach 15 Jahren hat sich die Einwohnerzahl verdoppelt. (a) Nehmen Sie lineares Wachstum gemäß z(t) = at + b an, wobei z die Einwohnerzahl ist und
QM: Prüfen -1- KN16.08.2010
 QM: Prüfen -1- KN16.08.2010 2.4 Prüfen 2.4.1 Begriffe, Definitionen Ein wesentlicher Bestandteil der Qualitätssicherung ist das Prüfen. Sie wird aber nicht wie früher nach der Fertigung durch einen Prüfer,
QM: Prüfen -1- KN16.08.2010 2.4 Prüfen 2.4.1 Begriffe, Definitionen Ein wesentlicher Bestandteil der Qualitätssicherung ist das Prüfen. Sie wird aber nicht wie früher nach der Fertigung durch einen Prüfer,
3. Verpackungskünstler. Berechnungen am Quader, Umgang mit Termen, räumliche Vorstellung
 Berechnungen am Quader, Umgang mit Termen, räumliche Vorstellung Päckchen, die man verschenken möchte, werden gerne mit Geschenkband verschnürt. Dazu wird das Päckchen auf seine größte Seite gelegt, wie
Berechnungen am Quader, Umgang mit Termen, räumliche Vorstellung Päckchen, die man verschenken möchte, werden gerne mit Geschenkband verschnürt. Dazu wird das Päckchen auf seine größte Seite gelegt, wie
VORANGEGANGENE MODELLE
 VORANGEGANGENE MODELLE UNSER THEMA HEUTE Ziel dieses Papers: - Nähere Charakterisierung der AuxREs - Analyse eines zu den AuxREs gehörenden Transkriptionsfaktors WAS BEREITS BEKANNT WAR: - Auxin moduliert
VORANGEGANGENE MODELLE UNSER THEMA HEUTE Ziel dieses Papers: - Nähere Charakterisierung der AuxREs - Analyse eines zu den AuxREs gehörenden Transkriptionsfaktors WAS BEREITS BEKANNT WAR: - Auxin moduliert
Protokoll des Versuches 7: Umwandlung von elektrischer Energie in Wärmeenergie
 Name: Matrikelnummer: Bachelor Biowissenschaften E-Mail: Physikalisches Anfängerpraktikum II Dozenten: Assistenten: Protokoll des Versuches 7: Umwandlung von elektrischer Energie in ärmeenergie Verantwortlicher
Name: Matrikelnummer: Bachelor Biowissenschaften E-Mail: Physikalisches Anfängerpraktikum II Dozenten: Assistenten: Protokoll des Versuches 7: Umwandlung von elektrischer Energie in ärmeenergie Verantwortlicher
Säure-Base-Titrationen
 Säure-Base-Titrationen Dieses Skript gehört: Säure Base - Titrationen Seite 2 Hinweis: Mit den Säuren und Basen ist vorsichtig umzugehen, um Verätzungen zu vermeiden! Versuch 1: Herstellen einer Natronlauge
Säure-Base-Titrationen Dieses Skript gehört: Säure Base - Titrationen Seite 2 Hinweis: Mit den Säuren und Basen ist vorsichtig umzugehen, um Verätzungen zu vermeiden! Versuch 1: Herstellen einer Natronlauge
Titration von Speise-Essig
 Titration von Speise-Essig Wir werden in diesem Versuch die Titration [frz.titer = Feingehalt] Konzentration der Essigsäure in Analytisches Verfahren, bei dem die Reagenzlösung tropfenweise zugesetzt wird,
Titration von Speise-Essig Wir werden in diesem Versuch die Titration [frz.titer = Feingehalt] Konzentration der Essigsäure in Analytisches Verfahren, bei dem die Reagenzlösung tropfenweise zugesetzt wird,
Bericht über die Untersuchung zur Erblichkeit von Herzerkrankungen beim PON
 1 Bericht über die Untersuchung zur Erblichkeit von Herzerkrankungen beim PON Einleitung Bei der Rasse PON wurden im APH in der letzten Zeit auffällig viele Herzkrankheiten und Herzveränderungen unterschiedlicher
1 Bericht über die Untersuchung zur Erblichkeit von Herzerkrankungen beim PON Einleitung Bei der Rasse PON wurden im APH in der letzten Zeit auffällig viele Herzkrankheiten und Herzveränderungen unterschiedlicher
