DNA Reparatur. Häufige Ursachen von DNA Schäden und ihre. Reparaturmechanismen. Syndrome mit defekter DNA-Reparatur
|
|
|
- Waltraud Schuler
- vor 8 Jahren
- Abrufe
Transkript
1 DNA Reparatur Häufige Ursachen von DNA Schäden und ihre Reparaturmechanismen Syndrome mit defekter DNA-Reparatur Karzinogene und ihre Wirkungsweise
2 Direkte Reparatur I: die meisten Fehler werden bei der Replikation gemacht und Mutationen trotzdem verhindert! Polymerase -Fehlerrate ~10(e -5) Korrekturlesen ~10(e -2) Fehlpaarungsreparatur ~10(e -3) Gesamt ~10(e -10)
3 UV-Licht kann benachbarte Pyrimidinreste im gleichen Strang crosslinken
4 Direkte Reparatur II: Bakterien und Hefen können Pyrimidindimere photochemisch spalten und zu zwei Monomeren rekonvertieren Die Photolyase besitzt ein Coenzym (N 5, N 10 -Methenyltetrahydrofolat), welches ein Photon absorbieren und dadurch angeregt werden kann.
5 Direkte Reparatur III: die Methylguaninmethyltransferase kann Methylierung von G (zu 6-O-MeG) rückgängig machen Wichtiger Mechanismus z.b. während einer Krebstherapie mit alkylierenden Chemotherapeutika; MGMT-Spiegel müssen dazu gesenkt werden (durch 6-O-Benzylguanin).
6 Desaminierung von C oder 5-Methyl-C ist die häufigste Ursache für Punktmutationen
7 Spontan desaminierte Basen werden durch die Basenexzisionsreparatur repariert NH 2 O O N HN HN CH 3 O N O N O N Cytosin (C) Uracil (U) Thymin (T) Andere DNA-Glykosylasen sind spezifisch für andere modifizierte Basen, z.b. 8-Oxy-Guanin. Depurinierung wird durch einen ähnlichen Mechanismus repariert.
8 Warum enthält RNA Uracil (bzw. warum enthält DNA Thymin)? Die Methylierung von Desoxyuridylat zu Desoxythymidylat ist energetisch aufwendig; was ist der Grund für diese Energieverschwendung? NH 2 O O N HN HN CH 3 O N O N O N Cytosin (C) Uracil (U) Thymin (T) Cytosin in der DNA desaminiert zu einem messbaren Prozentsatz spontan zu Uracil. Da Uracil mit Adenin paart, ist die Desaminierung potenziell mutagen (einer der Tochterstränge würde ein AU-Basenpaar statt einem CG Basenpaar enthalten). In DNA eingebautes Uracil wird durch ein spezielles Reparaturenzym entfernt. Die Methylmarkierung des Thymidins bewirkt, das Thymin von der Uracil-DNA-Glykosidase nicht erkannt wird. Wäre die Methylgruppe nicht vorhanden, könnte korrekt eingebautes Uracil nicht von durch Desaminierung gebildetem Uracil unterschieden werden.
9 UV-Licht kann benachbarte Pyrimidinreste im gleichen Strang crosslinken
10 Pyrimidindimere können durch die Nukleotidexzisionsreparatur repariert werden In E.coli: Nuklease=UvrABC-Excinuklease
11 Xeroderma pigmentosum Patienten haben Defekte in der Nukleotidexzisionsreparatur klinisch und genetisch heterogene Erbkrankheit Häufigkeit 1:10 5-1:10 6 Symptome Extreme Sensitivität gegenüber UV Strahlung 2000-fach erhöhtes Hautkrebsrisiko Schwere Haut- und Augenanomalien Neurologische Defekte (20% der Patienten) Lebenserwartung um 30 Jahre verkürzt
12 Die in XP-Patienten mutierten Gene führten zur Aufklärung der Wirkungsweise der Nukleotidexzisionsreparatur im Menschen 1. UV-Licht 4. Bildung des Reparaturkomplexes TFIIH XPB XPA XPD XPG 2. Schadenerkennung durch XPC RPA 23B XPC 5. Excision durch XPF und XPG Endonukleasen 3. Rekrutierung der Helikasen XPB, XPD ERCC1 XPA TFIIH 23B XPC XPF RPA XPG 6. Reparatursynthese (Pol ε)
13 XPV ist nicht beteiligt an Reparatur; es ist eine Polymerase, die Pyrimidindimere tolerieren und übergehen kann (by-pass-polymerase). Eukaryonten DNA-Pol α DNA-Pol β DNA-Pol γ DNA-Pol δ DNA-Pol ε DNA-Pol κ DNA-Pol λ DNA-Pol ι DNA-Pol θ DNA-Pol ϕ DNA-Pol η Primase, kurze DNA-Fragmente Reparatur Replikation des Mitochondriengenoms (16.6 kbp zirkulär*) Replikation Folgestrang Replikation Leitstrang DNA-Synthese auf beschädigter DNA " " " "
14 Verschiedene Arten von Mutationen treten bei der Replikation auf 1. Substitution eines Basenpaares durch ein anderes (am häufigsten) 2. Deletion eines oder mehrerer Basenpaare 3. Insertion eines oder mehrerer Basenpaare Transition: Ersatz eines Purins durch ein anderes oder eines Pyrimidins durch ein anderes Transversion: Ersatz eines Purins durch ein Pyrimidin oder umgekehrt
15 Die Fehlpaarungsreparatur erkennt fehlgepaarte Basen oder kleine Insertionen In E. coli: MutL rekrutiert die Endonuklease MutH, die den nicht-methylierten Strang (blau) spaltet.
16 5' 3' 3' Die Fehlpaarungsreparatur erkennt fehlgepaarte Basen oder kleine Insertionen G T 5' 5' 3' 3' G T hmlh1 hpms2 Exo1 5' hmsh6 G T hmsh2 5' 3' 3' ADP ATP 5' MutSα, MutLα Exo1, PCNA RPA 5' 3' 3' DNA polymerase δ / PCNA DNA ligase 5' 3' G 3' C 5' 5' 5' 3' 3' hmlh1 hpms2 5' ATP ADP hmlh1 hpms2 5' 3' 3' G T 5' Im Menschen: Der Mismatch-Erkennungskomplex aus MSH2/6 und MLH1/PMS2 wandert an der DNA entlang, bis er auf eine Strangdiskontinuität trifft. Dort wird durch PMS2 ein Einzelstrangbruch eingeführt und Exo1 rekrutiert, die den Tochterstrang abbaut.
17 Ionisierende Strahlung (X-, γ ) kann Doppelstrangbrüche hervorrufen
18 Diese werden durch nicht-homologes End-joining repariert
19 Doppelstrangbrüche können auch durch homologe Rekombination repariert werden
20 Doppelstrangbrüche können auch durch homologe Rekombination repariert werden
21 Die Fusion nicht-zusammenpassender Enden kann zu chromosomalen Translokationen und Krebs führen Die t(8;14) Translokation beim Burkitt-Lymphom bewirkt Űberexpression des Myc-Onkoproteins (Transkription von Cyclingenenverstärkte Zellteilung)
22 IgH und Bcl-2 fusionieren bei Follicularem Lymphom, was zu Bcl-2 Űberexpression fuehrt
23 Fehlerhaftes End-joining kann zu chromosomalen Translokationen und Krebs führen Bei der t(9;22) Translokation in CML- Patienten fusioniert der BCR- mit dem Abl- Lokus; Das Fusionsprodukt hat konstitutive Tyrosinkinaseaktivität.
24 Konstitutiv aktives BRC-ABL phosphoryliert zahlreiche neue Substrate und macht die Zellteilung unabhängig von Wachsumsfaktoren Imatinib (Gleevec) blockiert spezifisch BRC-ABL.
25 Der Nachweis von chromosomalen Translokationen erfolgt über FISH
26 Die Enden von Chromosomen replizieren mit Hilfe des Enzyms Telomerase
27 Stammzellen haben lange Telomere und viel Telomerase; in somatischen Zellen nimmt die Telomerlänge mit zunehmenden Alter ab und Telomerase fehlt
28 Der Verlust von Telomeren bewirkt Abbruch-Fusion-Brücken Zyklen (breakage-fusion-bridge cycles)
29 Karzinogene sind häufig Mutagene Epidemiologischer Zusammenhang zwischen Rauchen und Lungenkrebs
30 Benzo(a)pyren wird von Cytochrom P450 Enzymen aktiviert und modifiziert Guanin, so dass es mit A statt C paart (G->T Transversion) Kausaler Zusammenhang zwischen Rauchen und Lungenkrebs
31 Aflatoxin (ein Schimmelpilzgift) modifiziert nach Aktivierung ebenfalls G und bewirkt G-> T Transversionen (seltene Mutationen in p53)
32 Das Erhitzen von Fleisch bei hohen Temperaturen erzeugt heterozyklische Amine, die Guaninaddukte bilden und mit Prostatakrebs in Verbindung stehen (p53 Mutationen)
33 Erbkrankheiten mit DNA-Reparatur-Defekten
34 Expression der genetischen Information- RNA-Synthese (Transkription)
35 Bei der Transkription wird DNA in RNA umgeschrieben (transkribiert)
36 Einige Konventionen bei der Beschreibung der Transkription
37 Die Transkription besteht aus 3 Schritten: Initiation, Elongation und Termination
38
39
40 Űbersicht Transkription
41 Bakterien besitzen eine einzige RNA-Polymerase, die aus mehreren Untereinheiten besteht Untereinheit Gen Anz. Masse Funktion (kd)! rpo A 2 37 Bindet regulatorische Sequenzen " rpo B Bildet Phosphodiesterbindungen " rpo C Bindet die DNA-Matrize # 70 rpo D 1 70 Erkennt den Promotor und initiiert die Synthese
42 Bakt. RNA-Polymerase mit Matrize während der Elongation Transkriptionsrichtung
43 Bakterielle und eukaryotische RNA-Polymerasen sind ähnlich aufgebaut
44 Eukaryoten besitzen mehrere RNA-Polymerasen mit unterschiedlicher Funktion
45 Die Zusammensetzung der Untereinheiten ist bei allen RNA-Pol ähnlich
46 Nur die RNA-Pol II (mrna Synthese) hat eine C-terminale Domäne, die während aktiver Transkription phosphoryliert wird chromosomal puffs : Orte aktiver Transkription grün: nicht-phosphorylierte CTD rot: phosphorylierte CTD
47 Genorganisation in Pro- und Eukaryoten
48 Transkription und Translation sind in Eukaryoten zeitlich und räumlich getrennt
49 Regulation der Genexpression-- Prokaryoten
50 Die Sigma-Untereinheit der bakt. RNA-Pol erkennt Promotorsequenzen upstream des Transkriptionsstarts -35 Region -10 Region TTGACAT bp TATAAT
51 E. coli kann die Gene des Laktosemetabolismus in Abhängigkeit von Substratverfügbarkeit kontrollieren Die Kontrollregion rund um den Transkriptionsstart des lacz-operons besteht aus ca. 100bp, die Repressoren und Aktivatoren binden
52 RNA-Pol assoziiert mit unterschiedlichen Sigmafaktoren, je nach Wachstumsphase und Substratverfügbarkeit housekeeping heat shock nitrogen metabolism
53 Transkriptionsfaktoren können auch sehr weit entfernt vom Transkriptionsstart an regulatorische Sequenzen binden- sog. Enhancer Schleifenbildung
54 Zwei-Komponentensysteme erlauben es Bakterien, schnell auf Umwelteinflüsse zu reagieren
55 Regulation der Genexpression-- Eukaryoten
56 Eukaryotische RNA-Pol erkennen ebenfalls Promotorsequenzen upstream des Transkriptionsstarts
57 Konsensussequenz der TATA-Box >900 eukaryotische Gene analysiert
58 Die generellen Transkriptionsfaktoren TFIIA,B, und D ermöglichen die Initiation der Transkription durch sukzessive Bindung an die TATA-Box
59 Alternativ zur TATA-Box können Initiator-Elemente oder CpG- Inseln als Promotoren (z.b. von housekeeping-genen) dienen Initiator 5 - Y-Y-A +1 -N-T/A-Y-Y-Y -3 CpG Insel
60 Typischer Aufbau eines Säuger- bzw. Hefegenlokus-- Enhancer können viele kb upstream vom durch sie regulierten Gen liegen
61 Die Kontrollregion eines Gens kann Bindungsstellen (Enhancerelemente) für mehrere Transkriptionsfaktoren haben
62 Enhancer werden von Transkriptionsfaktoren gebunden, die eine DNA-Bindungs- und eine Aktivierungsdomäne besitzen
63 Die DNA-Bindungsdomäne eines Transkriptionsfaktors interagiert mit DNA (grosse Furche) z.b. mittels einer α-helix
64 Viele Transkriptionsfaktoren haben Zink-Finger-Domänen, die ebenfalls eine α-helix in die grosse Furche inserieren GL1: C 2 H 2, monomeric Glucocorticoid-R: C 4, homodimeric; recognizes inverted repeats
65 Andere Transkriptionsfaktoren gehören zur Familie der Leucine-Zipper- oder Helix-Loop-Helix-Proteine Leucine Zipper Basic Helix loop Helix Im C-Terminus bewirken hydrophobe AS die Dimerisierung (amphipathische α- Helices) Im N-Terminus bewirken positiv geladene (basische) AS die Bindung an DNA (Phosphatreste)
66 Manche Transkriptionsfaktoren brauchen die Hilfe von Co-Aktivatoren Der Östrogenrezeptor gehört zur Transkriptionsfaktor- Familie der nuclear receptors.
67 Manche Transkriptionsfaktoren kooperieren : nur wenn beide vorhanden sind, können AP1 und NFAT hochaffin an promotor-proximale Kontrollelemente binden IL-2 Genlokus
68 An Enhancerelementen bilden sich häufig Multiproteinkomplexe (Enhancesomen), die kooperativ die Genexpression regulieren β-interferon Enhancerelement
69 Wie werden Transkriptionsfaktoren reguliert? -Entwicklungsspezifische Regulation -Zelltyp-/Gewebe-/Organspezifische Regulation -Regulation durch Signale von aussen: Proteinsignale Hormonsignale
70 Steroidhormone wirken, indem sie spezifische Transkriptionsfaktoren ( nuclear receptors ) aktivieren
71 Nuclear receptors haben konservierte DNA-Bindungsdomänen und variable N- und C-Termini
72 Manche Nuclear receptors binden als Homodimere, andere als Heterodimere an ihre Kontrollregionen (Response elements) Der Glukocorticoid- und der Östrogenrezeptor binden als Homodimere an inverted repeats. Die Vitamin D3-, Thyroxin- und Retinolsäurerezeptoren bilden Heterodimere mit RXR, und binden an direkte repeats, die sich nur in der Anzahl zwischengeschalteter Nukleotide unterscheiden (N) 3,4,5.
73 Hormonbindung aktiviert die homodimeren Nuclear receptors, indem sie ihre Translokation vom Zytoplasma in den Kern induziert - Hormon + Hormon
74 Wie arbeiten Transkriptionsfaktoren? -beeinflussen die Dichte des Chromatins und damit die Zugänglichkeit der DNA für Proteine -regulieren die Initiation der Transkription, indem sie die Zusammenlagerung des Präinitiationskomplexes bewirken
75 Transkriptionsfaktoren wie z.b. die Nuclear Rezeptors wirken, indem sie die Packung der DNA beeinflussen
76 Aktiv transkribierte Gene befinden sich in lose gepacktem (Eu)chromatin
77 Die Kondensation des Chromatins wird durch Acetylierung von Histonen beeinflusst Reprimierende bzw. aktivierende Transkriptionsfaktoren beeinflussen den Acetylierungsstatus benachbarter Nukleosomen und damit die Zugänglichkeit der in ihnen verpackten Promotorsequenzen
78 Methylcytosin in CG-Dinukleotiden kann ebenfalls durch Rekrutierung von Histon-Deacetylasen Chromatinkondensation bewirken 5-Methylcytosin NH 2 CH 3 O N N 5 T T A A C G A T A C 3 3 A A T T G C T A T G 5
79 Sukzessive Bindung der generellen Transkriptionsfaktoren an Promotorelemente initiiert die Transkription
80 Pol II im Komplex mit DNA und generellen Transkriptionsfaktoren
81 Der Mediatorkomplex rekrutiert Pol II an Promotoren, indem er sowohl an Pol II als auch an Aktivierungsdomänen von Transkriptionsfaktoren bindet
82 Die Elongation verläuft hochprozessiv mit 50 Nukleotiden/ Sekunde Die Entwindung der DNA in der Transkriptionsblase wird von TFIIH Vorangetrieben.
83 In Prokaryoten besteht das Terminationssignal aus einer Haarnadelschleife gefolgt von einer poly-u Sequenz
84 In Eukaryoten wird das Primärtranskript prozessiert
85 Übersicht über Primärtranskript-Prozessierung in Eukaryoten
86 Die Prä-mRNA erhält ko-transkriptionell ein schützendes Cap Das capping Enzym bindet an die phosphorylierte CTD der PolII und wird dadurch aktiviert
87 Die Prä-mRNA erhält post-transkriptionell einen poly(a)-schwanz
88 EM-Fotos von mrna-dna-hybriden bewiesen die Existenz von Introns
89 Übersicht über RNA-Prozessierung inkl. Spleissen
90 Konsensus-Sequenz der Spleiss-Region
91 Atomarer Mechanismus des Spleissens
92 Am Spleissprozess sind ca. 100 Proteine und 5 snrnas beteiligt Im ersten Schritt hybridisieren die U1 und U2 snrnas mit der 5 Spleissstelle und der Sequenz um die Verzweigungsstelle
93 Das nicht gepaarte A der Verzweigungsstelle zeigt aus dem Hybrid der U2 snrna mit der komplementären Sequenz der Prä-mRNA heraus
94 Durch anschliessende Anlagerung der U4-6 Ribonukleoproteinkomplexe entsteht das Spleissosom
95 Die U2 und U6 Ribonukleoproteinkomplexe bilden das katalytische Zentrum Bei der ersten Transesterifizierung bildet sich ein 2-5 verknüpftes Intermediat zwischen dem G am 5 des Introns und dem A der Verzweigungsstelle Die beiden Exons werden bei der zweiten Transesterifizierung über eine normale 5-3 Verknüpfung verbunden Nach extensiver Umlagerung der Basenpaarungen zwischen U1,2,4,5 und 6 dissoziieren U1 und U4 ab.
96 Vorgang des Spleissens
97 Die snrnas im Spleissosom leiten sich wahrscheinlich von sich selbst spleissenden Introns ab
98 Durch die Assoziation von mrna-prozessierenden Proteinen mit phosphorylierter CTD von PolII werden Transkription und Prozessierung gekoppelt
99 Übersicht Transkription, mrna-prozessierung und Translation
100 Ribosomale RNA (rrna) wird als eine einzige Prä-rRNA synthetisiert
101 Pro Transkriptionseinheit werden simultan zahlreiche Prä-rRNA- Moleküle von RNA-Pol I synthetisiert
102 rrna wird in Nukleoli transkribiert, und assoziiert sofort mit ribosomalen Proteinen
103 Ribosomen sind Nukleoprotein-Komplexe und bestehen zu 60% aus RNA und zu 40% aus Protein
104 Bei der Reifung der Prä-rRNA im Nukleolus wird das Primärtranskript exo- und endonukleolytisch gespalten und methyliert
105 Jede trna ist spezifisch für eine Aminosäure, die am 3 -Ende gebunden wird trnas bestehen aus ca. 75 Nukleotiden, die teilweise Basenpaarungen eingehen.
106 Auch trnas werden im Kern post-transkriptionell prozessiert Das 5 Ende wird exonukleolytisch durch RNase P gespalten. Die Uridin-Reste am 3 Ende werden durch CCA ersetzt. Etwa 10% der Nukleotide in trnas werden modifiziert. Manche trnas besitzen Introns, die herausgespleisst werden müssen.
107 Bei der Modifizierung der Basen entstehen einige seltene Nukleotide N N O N NH NH 2 Guanin (G) (G) NH 2 N N N N Adenin (A) (A) NH 2 O O N HN CH HN 3 O N O N O N Cytosin (C) Uracil (U) Thymin (T) O O NH 2 O - CH 3 HN N HN NH N CH 3 N N + N N O O N NH 2 N N Ribose Ribose Ribose Ribose Inosin (I) Pseudouridin (Ψ) 5 Methylcytosin (m5c) 7-Methylguanosin (m7g)
108 Die dreidimensionale Struktur einer trna sieht aus wie ein L
109 Translation/Proteinsynthese -Der genetische Code -Initiation, Elongation, Termination
110 Die drei Arten von RNA arbeiten bei der Proteinsynthese zusammen
111 Der genetische Code besteht aus 4 3 =64 Codons
112 Die meisten Aminosäuren werden durch mehr als 1 Codon spezifiziert
113 Die Abfolge von Codons zwischen einem Start- und einem Stopcodon heisst Leseraster (reading frame) Eine mrna kann für 2, in seltenen Fällen sogar 3 Polypeptide kodieren (Leserasterverschiebung).
114 Die Übersetzung der Nukleotidsequenz der mrna in die Aminosäuresequenz eines Proteins erfolgt in zwei Hauptschritten: 1. Die Aminosäure wird durch ihre spezifische Aminoacyl-tRNA-Synthetase an die korrespondierenden trnas gekoppelt.
115 Die Übersetzung der Nukleotidsequenz der mrna in die Aminosäuresequenz eines Proteins erfolgt in zwei Hauptschritten: 2. Das Anticodon der trna paart mit dem Codon in der mrna, das für die auf die trna geladene Aminosäure kodiert. Dadurch kann diese ins Protein eingebaut werden.
116 Die dritte Position eines Codons kann häufig mit mehr als einer Base im trna Anticodon paaren ( wobble position ) Beispiel: 4 der 6 für Leucin kodierenden Codons- CUA, CUC, CUU, UUAerkennen die gleiche trna (GAI), da das Inosin in der wobble position mit A, C und U paaren kann und das U in der Position 1 ein unkonventionelles Basenpaar mit G bilden kann.
117 Die Proteinsynthese erfolgt an der Schnittstelle zwischen kleiner und grosser Untereinheit der Ribosomen
118 Bakterielle (polycistronische) mrnas kodieren für mehrere Proteine, eukaryotische (monocistronische) mrnas nur für ein Protein
119 Die Proteinsynthese auf eukaryotischen mrnas beginnt in der Regel in <100 Nukleotiden Entfernung vom 5 Cap, am ersten AUG Kozak-Sequenz: ACCAUGG
120 Inaktive Ribosomenuntereinheiten sind separiert und an spezifische Initiationsfaktoren (IF) gebunden
121 Bei der Translationsinitiation in Eukaryoten muss sich zunächst ein Prä-Initiationskomplex aus kleiner Ribosomenuntereinheit, IFs und Methionyl-Initiator-tRNA bilden Regulation der Proteinsynthese über Phosphorylierung von eif2 (GDP-GTP-Austausch)
122 Der Prä-Initiationskomplex assoziiert dann mit mrna, an deren Cap eif4 gebunden hat, zum Initiationskomplex
123 Der Initiationskomplex wandert an der mrna entlang und sucht das Startkodon (scanning) Beim Scanning müssen RNA-Sekundärstrukturen durch die eif4a Helikase entwunden werden. Nachdem das Startkodon identifiziert worden und die trna über ihr Anticodon damit fest verbunden ist, hydrolysiert eif2-gtp zu GDP und alle IFs dissoziieren ab.
124 Unter Mithilfe von eif5 und 6 assoziiert am Startkodon die grosse Ribosomenuntereinheit mit der kleinen Untereinheit zum 80S Ribosom Dabei wird die Initiator-tRNA in der P-Stelle positioniert.
125 Die Proteinsynthese auf prokaryotischen mrnas beginnt an internen Startkodons, denen eine Shine-Dalgarno-Sequenz vorausgeht Die Shine-Dalgarno-Sequenz (6 bp, purinreich) ist komplementär zum 3 Ende der rrna in der kleinen Ribosomenuntereinheit.
126 Prokaryotischen mrnas haben kein Cap; der Initiationskomplex entsteht am Startkodon/ der Shine-Dalgarno-Sequenz
127 Die Elongation der Peptidkette wird durch Bindung einer neuen, komplementaren trna in Position A eingeleitet Die trnas sind an den Elongationsfaktor EF1α gebunden, der sie ans Ribosom transportiert
128 Die GTPase-Aktivität der Elongationsfaktoren stellt die Irreversibilität der einzelnen Schritte sicher Bei korrekter Basenpaarung hydrolysiert EF1α GTP zu GDP, was im Ribosom zu einer Konformationsänderung, und zu fester Bindung der trna führt Die 23S rrna (grosse Ribosomen-UE) katalysiert die Bildung einer Peptidbindung zwischen den Aminosäuren in Positionen A und P Nach erfolgter Peptidbindung treibt die Hydrolyse von GTP durch EF2 die Translokation des Ribosoms um ein Codon in 3 Richtung an
129 Elongation der Polypeptidkette-Mechanismus
130 Wie kann EF1α-GTP regeneriert werden? Eukaryoten EF1α EF1βγ EF2 Prokaryoten EF-Tu EF-T (GDP-GTP exchange factor) EF-G
131 Modell basierend auf cryoelektronenmikroskopischen Aufnahmen
132 Termination der Proteinsynthese erf1 erkennt Stopcodons UAA, UGA, UAG (Form von erf1 ist ähnlich wie trna) Abspaltung der fertigen Polypeptidkette ist gekoppelt an GTP Hydrolyse an/durch erf3
133 Inaktive Ribosomenuntereinheiten werden separiert und binden wieder an ihre Initiationsfaktoren (IF)
134 Zahlreiche Ribosomen arbeiten simultan an der gleichen mrna (Polysomen)
135 PABPI vernetzt das 3 Poly-A-Ende der mrna mit dem 5 Cap, so dass freiwerdende Ribosomenuntereinheiten sofort wieder starten können
136 Manche Antibiotika hemmen spezifisch die Proteinsynthese in Bakterien Antibiotikum Streptomycin Tetracyclin Chloramphenicol Cycloheximid Erythromycin Puromycin Wirkung und andere Aminoglykoside hemmen die Initiation und verursachen Fehlablesungen der mrna (bei Prokaryoten) lagert sich an die 30S-Untereinheit an und hemmt die Bindung der Aminoacyl-tRNAs (bei Prokaryoten) hemmt die Peptidyltransferaseaktivität der 50S-Ribosomenuntereinheit (bei Prokaryoten) hemmt die Peptidyltransferaseaktivität der 60S-Ribosomenuntereinheit (bei Eukaryoten) lagert sich an die 50S-Untereinheit an und hemmt die Translokation (bei Prokaryoten) verursacht vorzeitigen Kettenabbruch, weil es als Analogon der Aminoacyl-tRNA wirkt (bei Prokaryoten und Eukaryoten)
137 Manche bakteriellen Toxine wirken, in dem sie die Proteinsynthese im Wirt inhibieren (Diphtherietoxin) Ein modifizierter Histidinrest in EF2 (Diphthamid) wird von Diphtherietoxin ADP-ribosyliert
138
139 Post-transkriptionale Regulation der Genexpression -RNA interference/silencing -RNA editing -Alternatives Spleissen
140 micrornas sind Nukleotide lang und verhindern die Translation ihrer komplementären Ziel-mRNA(s)
141 mirnas werden durch Prozessierung von Primärtranskripten gewonnen
142 Die Bindung von mehreren mirna/risc-komplexen an den 3 UTR einer mrna bewirkt Translationsinhibition
143 1000 menschliche mirnas regulieren ca. 1/3 aller Gene
144 Dicer prozessiert neben Prä-miRNAs auch lange, doppelsträngige RNA (z.b. viralen Ursprungs) zu kurzer, ds RNA mirna und sirna unterscheiden sich nicht in ihrer Struktur, wohl aber in ihrer Wirkung.
145 Der silencing complex (RISC) kann die Genexpression über zwei unterschiedliche Mechanismen ausschalten
146 sirna wird experimentell eingesetzt, um Expression eines Gens auszuschalten (knock-down)
147 Lokale bzw. systemische Applikation von sirna eröffnet neue therapeutische Anwendungen P2X3 sirna (Kationenkanal) bei neuropathischem Schmerz VEGF sirna gegen makulare Degeneration der Retina Fas/Caspase 8 sirna gegen Hepatitis HBV sirna gegen HBVinduzierte Hepatitis SARS/Influenza sirna gegen Lungen- Infektionen mit dsrna Viren
148 RNA editing erzeugt zwei unterschiedliche Proteine vom gleichen Primärtranskript in der Leber und im Darm
149 Einfache Transkriptionseinheiten (~40%) kodieren für nur eine Polypeptidkette
150 Komplexe Transkriptionseinheiten (60%) kodieren für >1 Polypeptid
151 Alternatives Spleissen ermöglicht die Produktion membranständiger und löslicher Antikörper vom gleichen Primärtranskript
152 Alternatives Spleissen ermöglicht die Produktion membranständiger und löslicher Antikörper vom gleichen Primärtranskript
153 Alternatives Spleissen ermöglicht die Produktion der Fibronektin-Isoformen in der extrazellulären Matrix und im Serum Exone IIIA und B kodieren für Domänen, die Fibronektin an die Zelloberfläche binden. Lösliches Fibronektin ist dagegen an der Blutgerinnung beteiligt.
154 Genetische Vielfalt: Genumordnung (Rekombination) -Homologe Rekombination -Ortsspezifische Rekombination -Transposons und Retrotransposons -Exon shuffling
155
156
157
158
159 Ortsspezifische Rekombination: Beispiel Antikörperdiversität
160 Die Spezifität eines Antikörpers wird durch seine hypervariable Region bestimmt
161 Die Antikörpervielfalt wird durch somatische Rekombination generiert im Menschen: 250 V-Gensegmente 15 D-Gensegmente 4 J-Gensegmente =45000 Kombinationen
162 Somatische Rekombination erfordert eine Signalsequenz
163 Kompatible Gensegmente lagern sich über ihre Signalsequenzen zusammen Die Rag-Rekombinasen stabilisieren den Komplex 12/23-Spacer-Regel: nur Signalsequenzen mit unterschiedlich langen Spacerregionen können sich zusammenlagern.
164 Die Rekombination in B-Zellen erfordert Rag-Proteine und Komponenten der nicht-homologen Endenverknüpfung Kompatible Gensegmente lagern sich über ihre Signalsequenzen zusammen Rag-Rekombinasen schneiden je einen Strang. Die Partnerstränge werden kovalent verbunden. Die Haarnadelschleifen gehen assymetrisch oder symmetrisch auf. Überhänge werden generiert und aufgefüllt. Ligase 4 und XRCC4 ligieren die beiden Enden. => Zusätzliche Diversität entsteht durch Einfüllen von Nukleotiden, die in der Originalsequenz nicht vorkommen.
165 Pro B-Zelle wird nur ein Antikörper produziert 1. Beide homologen Chromosomen rekombinieren zunächst die D- und J-Segmente der schweren Kette. 2. Die V-DJ-Rekombination erfolgt nur auf einem Chromosom. Die Nähe von V-Promoter und Enhancer bewirkt, dass das rekombinierte Gen abgelesen werden kann. Oberflächen- Expression der schweren Kette inhibiert die V-DJ-Rekombination auf dem anderen Chromosom. 3. Ist die erste V-DJ-Rekombination unproduktiv, rekombiniert das 2. Chromosom (4.). 5. Sind beide Rekombinationen unproduktiv, stirbt die B-Zelle.
166 Jede B-Zelle kann Antikörper verschiedener Klassen exprimieren, die durch die konstante Domäne definiert sind Keimbahn-DNA rearrangierte DNA
167 Aktivierte B-Zellen können die Produktion ihrer schweren Ketten umschalten (class switch recombination)
168 Mobile Elemente (Transposons) machen 45% des menschlichen Genoms aus 45%
169 Transposons können über DNA- oder RNA-Intermediate im Genom springen (cut-and-paste vs. copy-and-paste-strategie) Retrotransposons vermehren sich bei jedem Transpositionsereignis.
170 DNA-Transposons vermehren sich nur, wenn sie in der S-Phase des Zellzyklus von bereits kopierten in nicht-kopierte Regionen springen Dieser auf den ersten Blick ineffiziente Mechanismus hat zu immerhin schon Kopien (3% der DNA) im menschlichen Genom geführt.
171 In Bakterien kommen nur DNA-Transposons vor- sie heissen IS (insertion sequence)-elemente Die invertierten Wiederholungen werden von der Transposase erkannt. Die direkten Wiederholungen an den Rändern entstehen beim Integration der Transposon-DNA in die Zielsequenz. Die zentrale Region kodiert für das Enzym Transposase.
172 Die Transposition von IS-Elementen erfolgt in 3 Schritten
173 Manche IS-Elemente können Antibiotikaresistenzen transportieren
174 LTR-Retrotransposons ähneln Retroviren, die ihr Genom ins Wirtsgenom integriert haben kodiert für reverse Transkriptase und Integrase LTR-Retrotransposons besitzen neben den kurzen zusätzlich lange direkte Wiederholungen, die für Promotor und Polyadenylierungsstelle kodieren.
175 LTR-Retrotransposons replizieren vermutlich wie Retroviren unter Ausnutzung von zellulären Enzymen
176 Die RT der LTR Retroposons schreibt das RNA-Intermediat in ds DNA um, die dann von Integrase ins Genom eingebaut werden kann
177 Lebenszyklus von Retroviren zum Vergleich
178 Non-LTR-Retrotransposons machen 34% des menschlichen Genoms aus
179 Non-LTR-Retrotransposons werden durch RNA-Pol von einem Promotor in der A/T-reichen Region abgelesen und im Cytoplasma translatiert Orf1 kodiert für ein RNA-bindendes Protein Orf2 kodiert für Reverse Transkriptase/DNA-Endonuklease SINEs sind nicht-kodierende Parasiten von LINEs.
180 In den Kern zurücktransportierte LINE RNA wird im Zuge der reversen Transkription ins Genom integriert
181 Zelluläre Enzyme bauen das RNA-Intermediat ab und füllen die Lücken auf
182 Integration von LINEs in protein-kodierende Sequenzen ist der Auslöser für einige Krankheiten ( % aller Mutationen) Faktor IX: Hämophilie B (Bluterkrankheit; 30% der Fälle spontan) Dystrophin: Duchenne Muskeldystrophie; (30% der Fälle spontan)
183 Mobile Elemente haben die Evolution eukaryotischer Organismen massgeblich vorangetrieben: Bsp. Exonverdoppelungen während der Meiose durch ungleichen Crossover L1: LINE Familie, die die Fähigkeit zur Transposition beibehalten hat.
184 Genverdoppelungen ermöglichten die Diversifizierung der β-globinfamilie
185 Exon shuffling : Austausch von Exons zwischen verschiedenen Genen durch homologe Rekombination (Doppel-Crossover) Alu: häufigster Typ von SINE.
186 Exon shuffling : Insertion eines fremden Exons durch Transposition benachbarter homologer DNA-Transposons
187 Exon shuffling : Insertion eines fremden Exons durch Überspringen eines schwachen LINE-Polyadenylierungssignals
DNA Replikation ist semikonservativ. Abb. aus Stryer (5th Ed.)
 DNA Replikation ist semikonservativ Entwindung der DNA-Doppelhelix durch eine Helikase Replikationsgabel Eltern-DNA Beide DNA-Stränge werden in 5 3 Richtung synthetisiert DNA-Polymerasen katalysieren die
DNA Replikation ist semikonservativ Entwindung der DNA-Doppelhelix durch eine Helikase Replikationsgabel Eltern-DNA Beide DNA-Stränge werden in 5 3 Richtung synthetisiert DNA-Polymerasen katalysieren die
8. Translation. Konzepte: Translation benötigt trnas und Ribosomen. Genetischer Code. Initiation - Elongation - Termination
 8. Translation Konzepte: Translation benötigt trnas und Ribosomen Genetischer Code Initiation - Elongation - Termination 1. Welche Typen von RNAs gibt es und welches sind ihre Funktionen? mouse human bacteria
8. Translation Konzepte: Translation benötigt trnas und Ribosomen Genetischer Code Initiation - Elongation - Termination 1. Welche Typen von RNAs gibt es und welches sind ihre Funktionen? mouse human bacteria
Expression der genetischen Information Skript: Kapitel 5
 Prof. A. Sartori Medizin 1. Studienjahr Bachelor Molekulare Zellbiologie FS 2013 12. März 2013 Expression der genetischen Information Skript: Kapitel 5 5.1 Struktur der RNA 5.2 RNA-Synthese (Transkription)
Prof. A. Sartori Medizin 1. Studienjahr Bachelor Molekulare Zellbiologie FS 2013 12. März 2013 Expression der genetischen Information Skript: Kapitel 5 5.1 Struktur der RNA 5.2 RNA-Synthese (Transkription)
RNA und Expression RNA
 RNA und Expression Biochemie RNA 1) Die Transkription. 2) RNA-Typen 3) RNA Funktionen 4) RNA Prozessierung 5) RNA und Proteinexpression/Regelung 1 RNA-Typen in E. coli Vergleich RNA-DNA Sequenz 2 Die Transkriptions-Blase
RNA und Expression Biochemie RNA 1) Die Transkription. 2) RNA-Typen 3) RNA Funktionen 4) RNA Prozessierung 5) RNA und Proteinexpression/Regelung 1 RNA-Typen in E. coli Vergleich RNA-DNA Sequenz 2 Die Transkriptions-Blase
Bei der Translation wird die Aminosäuresequenz eines Polypeptids durch die Sequenz der Nukleotide in einem mrna- Molekül festgelegt
 Bei der Translation wird die Aminosäuresequenz eines Polypeptids durch die Sequenz der Nukleotide in einem mrna- Molekül festgelegt 5 mrna Nukleotid 3 N-Terminus Protein C-Terminus Aminosäure Es besteht
Bei der Translation wird die Aminosäuresequenz eines Polypeptids durch die Sequenz der Nukleotide in einem mrna- Molekül festgelegt 5 mrna Nukleotid 3 N-Terminus Protein C-Terminus Aminosäure Es besteht
Eukaryotische messenger-rna
 Eukaryotische messenger-rna Cap-Nukleotid am 5 -Ende Polyadenylierung am 3 -Ende u.u. nicht-codierende Bereiche (Introns) Spleißen von prä-mrna Viele Protein-codierende Gene in Eukaryoten sind durch nicht-codierende
Eukaryotische messenger-rna Cap-Nukleotid am 5 -Ende Polyadenylierung am 3 -Ende u.u. nicht-codierende Bereiche (Introns) Spleißen von prä-mrna Viele Protein-codierende Gene in Eukaryoten sind durch nicht-codierende
Posttranskriptionale RNA-Prozessierung
 Posttranskriptionale RNA-Prozessierung Spaltung + Modifikation G Q Spleissen + Editing U UUU Prozessierung einer prä-trna Eukaryotische messenger-rna Cap-Nukleotid am 5 -Ende Polyadenylierung am 3 -Ende
Posttranskriptionale RNA-Prozessierung Spaltung + Modifikation G Q Spleissen + Editing U UUU Prozessierung einer prä-trna Eukaryotische messenger-rna Cap-Nukleotid am 5 -Ende Polyadenylierung am 3 -Ende
Musterlösung - Übung 5 Vorlesung Bio-Engineering Sommersemester 2008
 Aufgabe 1: Prinzipieller Ablauf der Proteinbiosynthese a) Erklären Sie folgende Begriffe möglichst in Ihren eigenen Worten (1 kurzer Satz): Gen Nukleotid RNA-Polymerase Promotor Codon Anti-Codon Stop-Codon
Aufgabe 1: Prinzipieller Ablauf der Proteinbiosynthese a) Erklären Sie folgende Begriffe möglichst in Ihren eigenen Worten (1 kurzer Satz): Gen Nukleotid RNA-Polymerase Promotor Codon Anti-Codon Stop-Codon
Die DNA Replikation. Exakte Verdopplung des genetischen Materials. Musterstrang. Neuer Strang. Neuer Strang. Eltern-DNA-Doppelstrang.
 Die DNA Replikation Musterstrang Neuer Strang Eltern-DNA-Doppelstrang Neuer Strang Musterstrang Exakte Verdopplung des genetischen Materials Die Reaktion der DNA Polymerase 5`-Triphosphat Nächstes Desoxyribonucleosidtriphosphat
Die DNA Replikation Musterstrang Neuer Strang Eltern-DNA-Doppelstrang Neuer Strang Musterstrang Exakte Verdopplung des genetischen Materials Die Reaktion der DNA Polymerase 5`-Triphosphat Nächstes Desoxyribonucleosidtriphosphat
Überblick von DNA zu Protein. Biochemie-Seminar WS 04/05
 Überblick von DNA zu Protein Biochemie-Seminar WS 04/05 Replikationsapparat der Zelle Der gesamte Replikationsapparat umfasst über 20 Proteine z.b. DNA Polymerase: katalysiert Zusammenfügen einzelner Bausteine
Überblick von DNA zu Protein Biochemie-Seminar WS 04/05 Replikationsapparat der Zelle Der gesamte Replikationsapparat umfasst über 20 Proteine z.b. DNA Polymerase: katalysiert Zusammenfügen einzelner Bausteine
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr
 Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
Dr. Jens Kurreck. Otto-Hahn-Bau, Thielallee 63, Raum 029 Tel.: 83 85 69 69 Email: jkurreck@chemie.fu-berlin.de
 Dr. Jens Kurreck Otto-Hahn-Bau, Thielallee 63, Raum 029 Tel.: 83 85 69 69 Email: jkurreck@chemie.fu-berlin.de Prinzipien genetischer Informationsübertragung Berg, Tymoczko, Stryer: Biochemie 5. Auflage,
Dr. Jens Kurreck Otto-Hahn-Bau, Thielallee 63, Raum 029 Tel.: 83 85 69 69 Email: jkurreck@chemie.fu-berlin.de Prinzipien genetischer Informationsübertragung Berg, Tymoczko, Stryer: Biochemie 5. Auflage,
Klausur zur Vorlesung Biochemie III im WS 2000/01
 Klausur zur Vorlesung Biochemie III im WS 2000/01 am 15.02.2001 von 15.30 17.00 Uhr (insgesamt 100 Punkte, mindestens 40 erforderlich) Bitte Name, Matrikelnummer und Studienfach unbedingt angeben (3 1.
Klausur zur Vorlesung Biochemie III im WS 2000/01 am 15.02.2001 von 15.30 17.00 Uhr (insgesamt 100 Punkte, mindestens 40 erforderlich) Bitte Name, Matrikelnummer und Studienfach unbedingt angeben (3 1.
Übung 11 Genregulation bei Prokaryoten
 Übung 11 Genregulation bei Prokaryoten Konzepte: Differentielle Genexpression Positive Genregulation Negative Genregulation cis-/trans-regulation 1. Auf welchen Ebenen kann Genregulation stattfinden? Definition
Übung 11 Genregulation bei Prokaryoten Konzepte: Differentielle Genexpression Positive Genregulation Negative Genregulation cis-/trans-regulation 1. Auf welchen Ebenen kann Genregulation stattfinden? Definition
Translation benötigt trnas und Ribosomen. Genetischer Code. Initiation Elongation Termination
 8. Translation Konzepte: Translation benötigt trnas und Ribosomen Genetischer Code Initiation Elongation Termination 1. Welche Typen von RNAs gibt es und welches sind ihre Funktionen? mouse huma n bacter
8. Translation Konzepte: Translation benötigt trnas und Ribosomen Genetischer Code Initiation Elongation Termination 1. Welche Typen von RNAs gibt es und welches sind ihre Funktionen? mouse huma n bacter
Translation benötigt trnas und Ribosomen. Genetischer Code. Initiation Elongation Termination
 8. Translation Konzepte: Translation benötigt trnas und Ribosomen Genetischer Code Initiation Elongation Termination 1. Welche Typen von RNAs gibt es und welches sind ihre Funktionen? mouse huma n bacter
8. Translation Konzepte: Translation benötigt trnas und Ribosomen Genetischer Code Initiation Elongation Termination 1. Welche Typen von RNAs gibt es und welches sind ihre Funktionen? mouse huma n bacter
Aufbau und Funktion des Genoms: Von der Genstruktur zur Funktion
 Assoc. Prof. PD Mag. Dr. Aufbau und Funktion des Genoms: Von der Genstruktur zur Funktion Wien, 2013 Währinger Straße 10, A-1090 Wien helmut.dolznig@meduniwien.ac.at www.meduniwien.ac.at/medizinische-genetik
Assoc. Prof. PD Mag. Dr. Aufbau und Funktion des Genoms: Von der Genstruktur zur Funktion Wien, 2013 Währinger Straße 10, A-1090 Wien helmut.dolznig@meduniwien.ac.at www.meduniwien.ac.at/medizinische-genetik
Expressionskontrolle in Eukaryonten
 Expressionskontrolle in Eukaryonten Warum muss Genexpression kontrolliert werden? 1. Gewebsspezifische Kontrolle - nicht jedes Genprodukt ist in allen Zellen erforderlich - manche Genprodukte werden ausschliesslich
Expressionskontrolle in Eukaryonten Warum muss Genexpression kontrolliert werden? 1. Gewebsspezifische Kontrolle - nicht jedes Genprodukt ist in allen Zellen erforderlich - manche Genprodukte werden ausschliesslich
Translation Teil 3 Proteinfaktoren und ihre Rolle in der Proteinsynthese
 Translation Teil 3 Proteinfaktoren und ihre Rolle in der Proteinsynthese Damit die Proteinsynthese beginnen kann, müssen m-rna und fmet-trna zum Ribosom gebracht werden. Wie geschieht das??? Von entscheidender
Translation Teil 3 Proteinfaktoren und ihre Rolle in der Proteinsynthese Damit die Proteinsynthese beginnen kann, müssen m-rna und fmet-trna zum Ribosom gebracht werden. Wie geschieht das??? Von entscheidender
Vom Gen zum Protein. Zusammenfassung Kapitel 17. Die Verbindung zwischen Gen und Protein. Gene spezifizieren Proteine
 Zusammenfassung Kapitel 17 Vom Gen zum Protein Die Verbindung zwischen Gen und Protein Gene spezifizieren Proteine Zellen bauen organische Moleküle über Stoffwechselprozesse auf und ab. Diese Prozesse
Zusammenfassung Kapitel 17 Vom Gen zum Protein Die Verbindung zwischen Gen und Protein Gene spezifizieren Proteine Zellen bauen organische Moleküle über Stoffwechselprozesse auf und ab. Diese Prozesse
Das zentrale Dogma der Molekularbiologie:
 Das zentrale Dogma der Molekularbiologie: DNA Transkription RNA Translation Protein 1 Begriffserklärungen GENOM: Ist die allgemeine Bezeichnung für die Gesamtheit aller Gene eines Organismus GEN: Ist ein
Das zentrale Dogma der Molekularbiologie: DNA Transkription RNA Translation Protein 1 Begriffserklärungen GENOM: Ist die allgemeine Bezeichnung für die Gesamtheit aller Gene eines Organismus GEN: Ist ein
Es ist die Zeit gekommen, zu verstehen, wie es zur Proteinbiosynthese kommt?! Wobei jeweils eine AS von 3 Basen codiert wird..
 Proteinbiosynthese Es ist die Zeit gekommen, zu verstehen, wie es zur Proteinbiosynthese kommt?! Alle Proteine, sind über die DNA codiert Wobei jeweils eine AS von 3 Basen codiert wird.. GENETISCHER CODE
Proteinbiosynthese Es ist die Zeit gekommen, zu verstehen, wie es zur Proteinbiosynthese kommt?! Alle Proteine, sind über die DNA codiert Wobei jeweils eine AS von 3 Basen codiert wird.. GENETISCHER CODE
Datenspeicherung und Datenfluß in der Zelle - Grundlagen der Biochemie
 Datenspeicherung und Datenfluß in der Zelle - Grundlagen der Biochemie Datenspeicherung und Datenfluß der Zelle Transkription DNA RNA Translation Protein Aufbau I. Grundlagen der organischen Chemie und
Datenspeicherung und Datenfluß in der Zelle - Grundlagen der Biochemie Datenspeicherung und Datenfluß der Zelle Transkription DNA RNA Translation Protein Aufbau I. Grundlagen der organischen Chemie und
6. DNA -Bakteriengenetik
 6. DNA -Bakteriengenetik Konzepte: Francis Crick DNA Struktur DNA Replikation Gentransfer in Bakterien Bakteriophagen 2. Welcher der folgenden Sätze entspricht der Chargaff-Regel? A) Die Menge von Purinen
6. DNA -Bakteriengenetik Konzepte: Francis Crick DNA Struktur DNA Replikation Gentransfer in Bakterien Bakteriophagen 2. Welcher der folgenden Sätze entspricht der Chargaff-Regel? A) Die Menge von Purinen
Biochemie Tutorium 9. RNA, Transkription
 Biochemie Tutorium 9 RNA, Transkription IMPP-Gegenstandskatalog 3 Genetik 3.1 Nukleinsäuren 3.1.1 Molekulare Struktur, Konformationen und Funktionen der Desoxyribonukleinsäure (DNA); Exon, Intron 3.1.2
Biochemie Tutorium 9 RNA, Transkription IMPP-Gegenstandskatalog 3 Genetik 3.1 Nukleinsäuren 3.1.1 Molekulare Struktur, Konformationen und Funktionen der Desoxyribonukleinsäure (DNA); Exon, Intron 3.1.2
Biochemisches Grundpraktikum
 Biochemisches Grundpraktikum Dr. Ellen Hornung; Email: ehornun@gwdg.de; Tel: 39-5748 Einteilung der Praktikumsplätze: Eintragen in Listen am - Dienstag, 10.11.2009, von 12:00 13:00 - Freitag, 13.11.2009,
Biochemisches Grundpraktikum Dr. Ellen Hornung; Email: ehornun@gwdg.de; Tel: 39-5748 Einteilung der Praktikumsplätze: Eintragen in Listen am - Dienstag, 10.11.2009, von 12:00 13:00 - Freitag, 13.11.2009,
4 DNA-Reparatur - März 2009
 Page 1 of 6 GRUNDLAGEN DER MOLEKULARBIOLOGIE Prof. Dr. Anne Müller 4 DNA-Reparatur 4.1 Direkte Reparatur 4.2 Basenexcisionsreparatur 4.3 Nucleotidexcisionsreparatur 4.4 Fehlpaarungsreparatur 4.5 Strangbruchreparatur
Page 1 of 6 GRUNDLAGEN DER MOLEKULARBIOLOGIE Prof. Dr. Anne Müller 4 DNA-Reparatur 4.1 Direkte Reparatur 4.2 Basenexcisionsreparatur 4.3 Nucleotidexcisionsreparatur 4.4 Fehlpaarungsreparatur 4.5 Strangbruchreparatur
Klonierung von S2P Rolle der M19-Zellen. POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel
 Klonierung von S2P Rolle der M19-Zellen POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel Inhalt 1. Was ist eine humane genomische DNA-Bank? 2. Unterschied zwischen cdna-bank und genomischer DNA-Bank?
Klonierung von S2P Rolle der M19-Zellen POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel Inhalt 1. Was ist eine humane genomische DNA-Bank? 2. Unterschied zwischen cdna-bank und genomischer DNA-Bank?
GRUNDLAGEN DER MOLEKULARBIOLOGIE
 Page 1 of 7 GRUNDLAGEN DER MOLEKULARBIOLOGIE Prof. Dr. Anne Müller 6 Genetische Vielfalt / Gen-Umordnungen 6.1 RNA-Editing 6.2 Alternatives Spleissen 6.3 Gen-Umordnungen Wie kann die Zahl der Proteine
Page 1 of 7 GRUNDLAGEN DER MOLEKULARBIOLOGIE Prof. Dr. Anne Müller 6 Genetische Vielfalt / Gen-Umordnungen 6.1 RNA-Editing 6.2 Alternatives Spleissen 6.3 Gen-Umordnungen Wie kann die Zahl der Proteine
Q1 B1 KW 49. Genregulation
 Q1 B1 KW 49 Genregulation Transkription Posttranskription elle Modifikation Genregulation bei Eukaryoten Transkriptionsfaktoren (an TATA- Box) oder Silencer (verringert Transkription) und Enhancer (erhöht
Q1 B1 KW 49 Genregulation Transkription Posttranskription elle Modifikation Genregulation bei Eukaryoten Transkriptionsfaktoren (an TATA- Box) oder Silencer (verringert Transkription) und Enhancer (erhöht
Von der DNA zum Eiweißmolekül Die Proteinbiosynthese. Ribosom
 Von der DNA zum Eiweißmolekül Die Proteinbiosynthese Ribosom Wiederholung: DNA-Replikation und Chromosomenkondensation / Mitose Jede Zelle macht von Teilung zu Teilung einen Zellzyklus durch, der aus einer
Von der DNA zum Eiweißmolekül Die Proteinbiosynthese Ribosom Wiederholung: DNA-Replikation und Chromosomenkondensation / Mitose Jede Zelle macht von Teilung zu Teilung einen Zellzyklus durch, der aus einer
Translation. Auflesung- Proteinsynthese
 Translation Auflesung- Proteinsynthese Proteinsynthese DNA mrna Transkription elágazási hely Translation Polypeptid Vor dem Anfang Beladen der trnas spezifische Aminosäure + spezifische trna + ATP Aminoacyl-tRNA
Translation Auflesung- Proteinsynthese Proteinsynthese DNA mrna Transkription elágazási hely Translation Polypeptid Vor dem Anfang Beladen der trnas spezifische Aminosäure + spezifische trna + ATP Aminoacyl-tRNA
5 Expression der genetischen Information - März 2009
 Page 1 of 21 GRUNDLAGEN DER MOLEKULARBIOLOGIE Prof. Dr. Anne Müller 5 Expression der genetischen Information 5.1 Struktur der RNA 5.2 RNA-Synthese (Transkription) 5.3 RNA-Polymerase 5.4 Promotoren 5.5
Page 1 of 21 GRUNDLAGEN DER MOLEKULARBIOLOGIE Prof. Dr. Anne Müller 5 Expression der genetischen Information 5.1 Struktur der RNA 5.2 RNA-Synthese (Transkription) 5.3 RNA-Polymerase 5.4 Promotoren 5.5
9.) Wie heißen die kurzen RNA-Moleküle, mit deren Hilfe die Polymerase die Replikation der DNA starten kann? a) Starter b) Primer c) Beginner
 Lernkontrolle M o d u l 1 A w i e... A n k r e u z e n! 1.) Wie viele Chromosomen besitzt eine menschliche Körperzelle? a) 23 b) 46 c) 44 2.) In welchem Zellorganell befindet sich die DNA? a) Zellkern
Lernkontrolle M o d u l 1 A w i e... A n k r e u z e n! 1.) Wie viele Chromosomen besitzt eine menschliche Körperzelle? a) 23 b) 46 c) 44 2.) In welchem Zellorganell befindet sich die DNA? a) Zellkern
Frage 1 A: Wieviele Codone des "Universellen genetisches Codes" kodieren:
 Frage 1 A: Wieviele Codone des "Universellen genetisches Codes" kodieren: Aminosäuren Translationsstart Translationsstop? B: Welche biochemische Reaktion wird von Aminoazyl-tRNA-Synthetasen katalysiert?
Frage 1 A: Wieviele Codone des "Universellen genetisches Codes" kodieren: Aminosäuren Translationsstart Translationsstop? B: Welche biochemische Reaktion wird von Aminoazyl-tRNA-Synthetasen katalysiert?
Molekularbiologie 6c Proteinbiosynthese. Bei der Proteinbiosynthese geht es darum, wie die Information der DNA konkret in ein Protein umgesetzt wird
 Molekularbiologie 6c Proteinbiosynthese Bei der Proteinbiosynthese geht es darum, wie die Information der DNA konkret in ein Protein umgesetzt wird 1 Übersicht: Vom Gen zum Protein 1. 2. 3. 2 Das Dogma
Molekularbiologie 6c Proteinbiosynthese Bei der Proteinbiosynthese geht es darum, wie die Information der DNA konkret in ein Protein umgesetzt wird 1 Übersicht: Vom Gen zum Protein 1. 2. 3. 2 Das Dogma
Proteinbiosynthese. Prof. Dr. Albert Duschl
 Proteinbiosynthese Prof. Dr. Albert Duschl DNA/RNA/Protein Im Bereich von Genen sind die beiden Stränge der DNA nicht funktionell äquivalent, weil nur einer der beiden Stränge transkribiert, d.h. in RNA
Proteinbiosynthese Prof. Dr. Albert Duschl DNA/RNA/Protein Im Bereich von Genen sind die beiden Stränge der DNA nicht funktionell äquivalent, weil nur einer der beiden Stränge transkribiert, d.h. in RNA
IV. Übungsaufgaben für die Jahrgangstufe 9 & 10
 IV. Übungsaufgaben für die Jahrgangstufe 9 & 10 Von der Erbanlage zum Erbmerkmal: 34) Welche Aufgaben haben Chromosomen? 35) Zeichne und benenne die Teile eines Chromosoms, wie sie im Lichtmikroskop während
IV. Übungsaufgaben für die Jahrgangstufe 9 & 10 Von der Erbanlage zum Erbmerkmal: 34) Welche Aufgaben haben Chromosomen? 35) Zeichne und benenne die Teile eines Chromosoms, wie sie im Lichtmikroskop während
3.5 Moderne Genetik - Vorgänge
 3.5 Moderne Genetik - Vorgänge Der genetische Code Jedes Gen besteht aus sogenannten Basentriplets. Das ist eine Sequenz von drei aufeinanderfolgenden Nukleinbasen, die für eine bestimmte Aminosäure stehen.
3.5 Moderne Genetik - Vorgänge Der genetische Code Jedes Gen besteht aus sogenannten Basentriplets. Das ist eine Sequenz von drei aufeinanderfolgenden Nukleinbasen, die für eine bestimmte Aminosäure stehen.
Zentrales Dogma der Biologie
 Zentrales Dogma der Biologie Transkription: von der DNA zur RNA Biochemie 01/1 Transkription Biochemie 01/2 Transkription DNA: RNA: Biochemie 01/3 Transkription DNA: RNA: Biochemie 01/4 Transkription RNA:
Zentrales Dogma der Biologie Transkription: von der DNA zur RNA Biochemie 01/1 Transkription Biochemie 01/2 Transkription DNA: RNA: Biochemie 01/3 Transkription DNA: RNA: Biochemie 01/4 Transkription RNA:
Kapitel 8 Ò Chromosomen und Genregulation
 Kapitel 8 Ò Chromosomen und Genregulation 8.1 Struktur eukaryontischer Chromosomen Ein menschlicher Zellkern ist nur zehn Mikrometer gross und (10-9 ) hat zwei Meter DNA drin. Damit es da kein Durcheinander
Kapitel 8 Ò Chromosomen und Genregulation 8.1 Struktur eukaryontischer Chromosomen Ein menschlicher Zellkern ist nur zehn Mikrometer gross und (10-9 ) hat zwei Meter DNA drin. Damit es da kein Durcheinander
Regulation der Genexpression: regulierbare Promotoren, Proteine und sirna
 Regulation der Genexpression: regulierbare Promotoren, Proteine und sirna Biochemie Praktikum Christian Brendel, AG Grez Ebenen der Genregulation in Eukaryoten Cytoplasma DNA Zellkern Introns Exons Chromatin
Regulation der Genexpression: regulierbare Promotoren, Proteine und sirna Biochemie Praktikum Christian Brendel, AG Grez Ebenen der Genregulation in Eukaryoten Cytoplasma DNA Zellkern Introns Exons Chromatin
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2014
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2014 Fragen für die Übungsstunde 8 (14.07-18.07.) 1) Von der DNA-Sequenz zum Protein Sie können
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2014 Fragen für die Übungsstunde 8 (14.07-18.07.) 1) Von der DNA-Sequenz zum Protein Sie können
Übung 8. 1. Zellkommunikation. Vorlesung Bio-Engineering Sommersemester 2008. Kapitel 4. 4
 Bitte schreiben Sie Ihre Antworten direkt auf das Übungsblatt. Falls Sie mehr Platz brauchen verweisen Sie auf Zusatzblätter. Vergessen Sie Ihren Namen nicht! Abgabe der Übung bis spätestens 05. 05. 08
Bitte schreiben Sie Ihre Antworten direkt auf das Übungsblatt. Falls Sie mehr Platz brauchen verweisen Sie auf Zusatzblätter. Vergessen Sie Ihren Namen nicht! Abgabe der Übung bis spätestens 05. 05. 08
KV: Translation Michael Altmann
 Institut für Biochemie und Molekulare Medizin KV: Translation Michael Altmann Herbstsemester 2008/2009 Übersicht VL Translation 1.) Genexpression 2.) Der genetische Code ist universell 3.) Punktmutationen
Institut für Biochemie und Molekulare Medizin KV: Translation Michael Altmann Herbstsemester 2008/2009 Übersicht VL Translation 1.) Genexpression 2.) Der genetische Code ist universell 3.) Punktmutationen
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 3. Aus welchen vier Nukleotiden ist RNA aufgebaut? 4. DNA RNA 5. Ein Wissenschaftler
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 3. Aus welchen vier Nukleotiden ist RNA aufgebaut? 4. DNA RNA 5. Ein Wissenschaftler
Träger der Erbinformation sind die Nukleinsäuren. Es handelt sich hierbei um hochmolekulare lineare Kettenmoleküle, die aus durch
 Achtung Die folgenden Texte sind als Stichworte für die Klausurvorbereitung zu sehen. Keinesfalls sind die Fragen in der Klausur auf den Inhalt dieser Folien beschränkt, sondern werden aus dem Stoff der
Achtung Die folgenden Texte sind als Stichworte für die Klausurvorbereitung zu sehen. Keinesfalls sind die Fragen in der Klausur auf den Inhalt dieser Folien beschränkt, sondern werden aus dem Stoff der
Elektronenmikroskopie zeigte die Existenz der A-, P- und E- trna-bindungsstellen. Abb. aus Stryer (5th Ed.)
 Elektronenmikroskopie zeigte die Existenz der A-, P- und E- trna-bindungsstellen Die verschiedenen Ribosomen-Komplexe können im Elektronenmikroskop beobachtet werden Durch Röntgenkristallographie wurden
Elektronenmikroskopie zeigte die Existenz der A-, P- und E- trna-bindungsstellen Die verschiedenen Ribosomen-Komplexe können im Elektronenmikroskop beobachtet werden Durch Röntgenkristallographie wurden
1. Beschriften Sie in der Abbildung die verschiedenen Bereiche auf der DNA und beschreiben Sie ihre Funktion! nicht-codogener Strang.
 ARBEITSBLATT 1 Transkription 1. Beschriften Sie in der Abbildung die verschiedenen Bereiche auf der DNA und beschreiben Sie ihre Funktion! Bindungsstelle für RNA-Polymerase RNA-Polymerase nicht-codogener
ARBEITSBLATT 1 Transkription 1. Beschriften Sie in der Abbildung die verschiedenen Bereiche auf der DNA und beschreiben Sie ihre Funktion! Bindungsstelle für RNA-Polymerase RNA-Polymerase nicht-codogener
Transkription Teil 2. - Transkription bei Eukaryoten -
 Transkription Teil 2 - Transkription bei Eukaryoten - Inhalte: Unterschiede in der Transkription von Pro- und Eukaryoten Die RNA-Polymerasen der Eukaryoten Cis- und trans-aktive Elemente Promotoren Transkriptionsfaktoren
Transkription Teil 2 - Transkription bei Eukaryoten - Inhalte: Unterschiede in der Transkription von Pro- und Eukaryoten Die RNA-Polymerasen der Eukaryoten Cis- und trans-aktive Elemente Promotoren Transkriptionsfaktoren
Zentrales Dogma der Biochemie Zyklus eines Retrovirus Der Fluss der genetischen Information verläuft von der DNA zur RNA zum Protein. Zumindest bis 19
 Unterschiede DNA < > RNA Posttranskriptionale Veränderungen EML BIORUNDE DNA/RNA II Zentrales Dogma der Biochemie Der Fluss der genetischen Information verläuft von der DNA zur RNA zum Protein. Outline
Unterschiede DNA < > RNA Posttranskriptionale Veränderungen EML BIORUNDE DNA/RNA II Zentrales Dogma der Biochemie Der Fluss der genetischen Information verläuft von der DNA zur RNA zum Protein. Outline
PROTEINBIOSYNTHESE "Das zentrale Dogma der Molekularbiologie"
 PROTEINBIOSYNTHESE "Das zentrale Dogma der Molekularbiologie" Die für die Synthese von Eiweißstoffen notwendigen Schritte sind: (1) Replikation der DNA: Vor jeder Zellteilung wird die gesamte zelluläre
PROTEINBIOSYNTHESE "Das zentrale Dogma der Molekularbiologie" Die für die Synthese von Eiweißstoffen notwendigen Schritte sind: (1) Replikation der DNA: Vor jeder Zellteilung wird die gesamte zelluläre
Anabole Prozesse in der Zelle
 Anabole Prozesse in der Zelle DNA Vermehrung RNA Synthese Protein Synthese Protein Verteilung in der Zelle Ziel: Zellteilung (Wachstum) und Differenzierung (Aufgabenteilung im Organismus). 2016 Struktur
Anabole Prozesse in der Zelle DNA Vermehrung RNA Synthese Protein Synthese Protein Verteilung in der Zelle Ziel: Zellteilung (Wachstum) und Differenzierung (Aufgabenteilung im Organismus). 2016 Struktur
Wiederholunng. Klassische Genetik
 Wiederholunng Klassische Genetik Mendelsche Regeln Uniformitätsregel Spaltungsregel Freie Kombinierbarkeit Koppelung von Genen Polygene: mehre Gene für ein Merkmal Pleiotropie: 1 Gen steuert mehrere Merkmale
Wiederholunng Klassische Genetik Mendelsche Regeln Uniformitätsregel Spaltungsregel Freie Kombinierbarkeit Koppelung von Genen Polygene: mehre Gene für ein Merkmal Pleiotropie: 1 Gen steuert mehrere Merkmale
Unterrichtsmaterialien in digitaler und in gedruckter Form. Auszug aus: Antibiotikaresistenz bei Pseudomonaden
 Unterrichtsmaterialien in digitaler und in gedruckter Form Auszug aus: Antibiotikaresistenz bei Pseudomonaden Das komplette Material finden Sie hier: School-Scout.de S 1 M 6 M 7 Erarbeitung II, Präsentation
Unterrichtsmaterialien in digitaler und in gedruckter Form Auszug aus: Antibiotikaresistenz bei Pseudomonaden Das komplette Material finden Sie hier: School-Scout.de S 1 M 6 M 7 Erarbeitung II, Präsentation
Verbesserte Basenpaarung bei DNA-Analysen
 Powered by Seiten-Adresse: https://www.gesundheitsindustriebw.de/de/fachbeitrag/aktuell/verbesserte-basenpaarungbei-dna-analysen/ Verbesserte Basenpaarung bei DNA-Analysen Ein Team aus der Organischen
Powered by Seiten-Adresse: https://www.gesundheitsindustriebw.de/de/fachbeitrag/aktuell/verbesserte-basenpaarungbei-dna-analysen/ Verbesserte Basenpaarung bei DNA-Analysen Ein Team aus der Organischen
Grundlegende Experimente der Molekulargenetik
 Übung 12 Wiederholung/Zusatzübung Inhalte: Mendelscher Erbgang Grundlegende Experimente der Molekulargenetik Transposons Methoden 1. Sie haben drei runde, gelbe Erbsen (A, B und C). Aus jeder der drei
Übung 12 Wiederholung/Zusatzübung Inhalte: Mendelscher Erbgang Grundlegende Experimente der Molekulargenetik Transposons Methoden 1. Sie haben drei runde, gelbe Erbsen (A, B und C). Aus jeder der drei
4. Genetische Mechanismen bei Bakterien
 4. Genetische Mechanismen bei Bakterien 4.1 Makromoleküle und genetische Information Aufbau der DNA Phasen des Informationsflusses Vergleich der Informationsübertragung bei Pro- und Eukaryoten 4.2 Struktur
4. Genetische Mechanismen bei Bakterien 4.1 Makromoleküle und genetische Information Aufbau der DNA Phasen des Informationsflusses Vergleich der Informationsübertragung bei Pro- und Eukaryoten 4.2 Struktur
In den Proteinen der Lebewesen treten in der Regel 20 verschiedene Aminosäuren auf. Deren Reihenfolge muss in der Nucleotidsequenz der mrna und damit
 In den Proteinen der Lebewesen treten in der Regel 20 verschiedene Aminosäuren auf. Deren Reihenfolge muss in der Nucleotidsequenz der mrna und damit in der Nucleotidsequenz der DNA verschlüsselt (codiert)
In den Proteinen der Lebewesen treten in der Regel 20 verschiedene Aminosäuren auf. Deren Reihenfolge muss in der Nucleotidsequenz der mrna und damit in der Nucleotidsequenz der DNA verschlüsselt (codiert)
AUFGABENSAMMLUNG Lösungen. Variabilität von Antikörpern 1
 Variabilität von Antikörpern 1 Rezeptoren bzw. Antikörper eines noch undifferenzierten B-Lymphocyten: a) Schreiben Sie die Anzahl der variablen Exons je Chromosom auf. b) Berechnen Sie die mögliche Anzahl
Variabilität von Antikörpern 1 Rezeptoren bzw. Antikörper eines noch undifferenzierten B-Lymphocyten: a) Schreiben Sie die Anzahl der variablen Exons je Chromosom auf. b) Berechnen Sie die mögliche Anzahl
DNA-Sequenzierung. Martina Krause
 DNA-Sequenzierung Martina Krause Inhalt Methoden der DNA-Sequenzierung Methode nach Maxam - Gilbert Methode nach Sanger Einleitung Seit 1977 stehen zwei schnell arbeitende Möglichkeiten der Sequenzanalyse
DNA-Sequenzierung Martina Krause Inhalt Methoden der DNA-Sequenzierung Methode nach Maxam - Gilbert Methode nach Sanger Einleitung Seit 1977 stehen zwei schnell arbeitende Möglichkeiten der Sequenzanalyse
Genaktivierung und Genexpression
 Genaktivierung und Genexpression Unter Genexpression versteht man ganz allgemein die Ausprägung des Genotyps zum Phänotyp einer Zelle oder eines ganzen Organismus. Genotyp: Gesamtheit der Informationen
Genaktivierung und Genexpression Unter Genexpression versteht man ganz allgemein die Ausprägung des Genotyps zum Phänotyp einer Zelle oder eines ganzen Organismus. Genotyp: Gesamtheit der Informationen
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
Foliensatz; Arbeitsblatt; Internet. Je nach chemischem Wissen können die Proteine noch detaillierter besprochen werden.
 03 Arbeitsauftrag Arbeitsauftrag Ziel: Anhand des Foliensatzes soll die Bildung und der Aufbau des Proteinhormons Insulin erklärt werden. Danach soll kurz erklärt werden, wie man künstlich Insulin herstellt.
03 Arbeitsauftrag Arbeitsauftrag Ziel: Anhand des Foliensatzes soll die Bildung und der Aufbau des Proteinhormons Insulin erklärt werden. Danach soll kurz erklärt werden, wie man künstlich Insulin herstellt.
Antwort: 2.Uracil. Antwort: 2. durch Wasserstoffverbindungen. Adenin, Cystein und Guanin kommen alle in der RNA und DNA vor.
 Antwort: 2.Uracil Adenin, Cystein und Guanin kommen alle in der RNA und DNA vor. Thymin kommt nur in der DNA vor; Uracil nimmt seinen Platz in den RNA- Molekülen ein. Antwort: 2. durch Wasserstoffverbindungen
Antwort: 2.Uracil Adenin, Cystein und Guanin kommen alle in der RNA und DNA vor. Thymin kommt nur in der DNA vor; Uracil nimmt seinen Platz in den RNA- Molekülen ein. Antwort: 2. durch Wasserstoffverbindungen
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
Begleittext zum Foliensatz Erbgänge beim Menschen
 Für ein besseres Verständnis der Folien werden vorab einige Begriffe definiert: Gen Genom Allel Ein Gen ist die physikalische und funktionelle Einheit der Vererbung. Biochemisch ist es eine geordnete Abfolge
Für ein besseres Verständnis der Folien werden vorab einige Begriffe definiert: Gen Genom Allel Ein Gen ist die physikalische und funktionelle Einheit der Vererbung. Biochemisch ist es eine geordnete Abfolge
Zeichen bei Zahlen entschlüsseln
 Zeichen bei Zahlen entschlüsseln In diesem Kapitel... Verwendung des Zahlenstrahls Absolut richtige Bestimmung von absoluten Werten Operationen bei Zahlen mit Vorzeichen: Addieren, Subtrahieren, Multiplizieren
Zeichen bei Zahlen entschlüsseln In diesem Kapitel... Verwendung des Zahlenstrahls Absolut richtige Bestimmung von absoluten Werten Operationen bei Zahlen mit Vorzeichen: Addieren, Subtrahieren, Multiplizieren
Versuch 8. Plasmid - Isolierung
 Versuch 8 Plasmid - Isolierung Protokollant: E-mail: Studiengang: Gruppen-Nr: Semester: Betreuer: Max Mustermann max@quantentunnel.de X X X C. Weindel & M. Schwarz Wird benotet?: Einleitung Ein Plasmid
Versuch 8 Plasmid - Isolierung Protokollant: E-mail: Studiengang: Gruppen-Nr: Semester: Betreuer: Max Mustermann max@quantentunnel.de X X X C. Weindel & M. Schwarz Wird benotet?: Einleitung Ein Plasmid
VORANGEGANGENE MODELLE
 VORANGEGANGENE MODELLE UNSER THEMA HEUTE Ziel dieses Papers: - Nähere Charakterisierung der AuxREs - Analyse eines zu den AuxREs gehörenden Transkriptionsfaktors WAS BEREITS BEKANNT WAR: - Auxin moduliert
VORANGEGANGENE MODELLE UNSER THEMA HEUTE Ziel dieses Papers: - Nähere Charakterisierung der AuxREs - Analyse eines zu den AuxREs gehörenden Transkriptionsfaktors WAS BEREITS BEKANNT WAR: - Auxin moduliert
APP-GFP/Fluoreszenzmikroskop. Aufnahmen neuronaler Zellen, mit freund. Genehmigung von Prof. Stefan Kins, TU Kaiserslautern
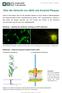 Über die Herkunft von Aβ42 und Amyloid-Plaques Heute ist sicher belegt, dass sich die amyloiden Plaques aus einer Vielzahl an Abbaufragmenten des Amyloid-Vorläufer-Proteins (amyloid-precursor-protein,
Über die Herkunft von Aβ42 und Amyloid-Plaques Heute ist sicher belegt, dass sich die amyloiden Plaques aus einer Vielzahl an Abbaufragmenten des Amyloid-Vorläufer-Proteins (amyloid-precursor-protein,
Transkription und Translation sind in Eukaryoten räumlich und zeitlich getrennt. Abb. aus Stryer (5th Ed.)
 Transkription und Translation sind in Eukaryoten räumlich und zeitlich getrennt Die Initiation der Translation bei Eukaryoten Der eukaryotische Initiationskomplex erkennt zuerst das 5 -cap der mrna und
Transkription und Translation sind in Eukaryoten räumlich und zeitlich getrennt Die Initiation der Translation bei Eukaryoten Der eukaryotische Initiationskomplex erkennt zuerst das 5 -cap der mrna und
Thema: Eukaryotische Genregulation und RNA- Prozessierung. Spleißen, Capping, Polyadenylierung, RNA-Editieren Erwin R. Schmidt 11. 01.
 Thema: Eukaryotische Genregulation und RNA- Prozessierung Spleißen, Capping, Polyadenylierung, RNA-Editieren Erwin R. Schmidt 11. 01. 2013 Worin unterscheiden sich die Gene bzw. die Genprodukte von Eukaryoten
Thema: Eukaryotische Genregulation und RNA- Prozessierung Spleißen, Capping, Polyadenylierung, RNA-Editieren Erwin R. Schmidt 11. 01. 2013 Worin unterscheiden sich die Gene bzw. die Genprodukte von Eukaryoten
Einführung Nukleinsäuren
 Einführung Nukleinsäuren Dr. Kristian M. Müller Institut für Biologie III Albert-Ludwigs-Universität Freiburg Einführung 1. Semester, WiSe 2007/2008 Historischer Überblick Literatur Bilder aus: Taschenatlas
Einführung Nukleinsäuren Dr. Kristian M. Müller Institut für Biologie III Albert-Ludwigs-Universität Freiburg Einführung 1. Semester, WiSe 2007/2008 Historischer Überblick Literatur Bilder aus: Taschenatlas
Eine neue RNA-Welt. Uralte RNA-Welt Am Anfang der Entstehung des Lebens. Bekannte RNA-Welt Protein-Synthese. Neue RNA-Welt Regulatorische RNA-Moleküle
 RNAs Eine neue RNA-Welt 1. Uralte RNA-Welt Am Anfang der Entstehung des Lebens Bekannte RNA-Welt Protein-Synthese Neue RNA-Welt Regulatorische RNA-Moleküle 2. Eine neue RNA-Welt die Anzahl der nicht-kodierenden
RNAs Eine neue RNA-Welt 1. Uralte RNA-Welt Am Anfang der Entstehung des Lebens Bekannte RNA-Welt Protein-Synthese Neue RNA-Welt Regulatorische RNA-Moleküle 2. Eine neue RNA-Welt die Anzahl der nicht-kodierenden
Anleitung über den Umgang mit Schildern
 Anleitung über den Umgang mit Schildern -Vorwort -Wo bekommt man Schilder? -Wo und wie speichert man die Schilder? -Wie füge ich die Schilder in meinen Track ein? -Welche Bauteile kann man noch für Schilder
Anleitung über den Umgang mit Schildern -Vorwort -Wo bekommt man Schilder? -Wo und wie speichert man die Schilder? -Wie füge ich die Schilder in meinen Track ein? -Welche Bauteile kann man noch für Schilder
Promotor kodierende Sequenz Terminator
 5.2 Genexpression Sequenz in eine RNA-Sequenz. Die Enzyme, die diese Reaktion katalysieren, sind die DNA-abhängigen RNA-Polymerasen. Sie bestehen aus mehreren Untereinheiten, die von den Pro- bis zu den
5.2 Genexpression Sequenz in eine RNA-Sequenz. Die Enzyme, die diese Reaktion katalysieren, sind die DNA-abhängigen RNA-Polymerasen. Sie bestehen aus mehreren Untereinheiten, die von den Pro- bis zu den
Weitergabe genetischer Information: DNA-Replikation Beispiel: Escherichia coli.
 Weitergabe genetischer Information: DNA-Replikation Beispiel: Escherichia coli. zirkuläres bakterielles Chromosom Replikation (Erstellung einer identischen Kopie des genetischen Materials) MPM 1 DNA-Polymerasen
Weitergabe genetischer Information: DNA-Replikation Beispiel: Escherichia coli. zirkuläres bakterielles Chromosom Replikation (Erstellung einer identischen Kopie des genetischen Materials) MPM 1 DNA-Polymerasen
AGROPLUS Buchhaltung. Daten-Server und Sicherheitskopie. Version vom 21.10.2013b
 AGROPLUS Buchhaltung Daten-Server und Sicherheitskopie Version vom 21.10.2013b 3a) Der Daten-Server Modus und der Tresor Der Daten-Server ist eine Betriebsart welche dem Nutzer eine grosse Flexibilität
AGROPLUS Buchhaltung Daten-Server und Sicherheitskopie Version vom 21.10.2013b 3a) Der Daten-Server Modus und der Tresor Der Daten-Server ist eine Betriebsart welche dem Nutzer eine grosse Flexibilität
Evolution & Genetik (Beispiel Hämoglobin) Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de
 Evolution & Genetik (Beispiel Hämoglobin) Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de DNA (Desoxyribonukleinsäure) 5 3 CGATGTACATCG GCTACATGTAGC 3 5 Doppelhelix Basen: Adenin,
Evolution & Genetik (Beispiel Hämoglobin) Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de DNA (Desoxyribonukleinsäure) 5 3 CGATGTACATCG GCTACATGTAGC 3 5 Doppelhelix Basen: Adenin,
PCD Europe, Krefeld, Jan 2007. Auswertung von Haemoccult
 Auswertung von Haemoccult Ist das positiv? Nein! Ja! Im deutschen Krebsfrüherkennungsprogramm haben nur etwa 1 % der Frauen und 1,5 % der Männer ein positives Haemoccult -Ergebnis, da dieser Test eine
Auswertung von Haemoccult Ist das positiv? Nein! Ja! Im deutschen Krebsfrüherkennungsprogramm haben nur etwa 1 % der Frauen und 1,5 % der Männer ein positives Haemoccult -Ergebnis, da dieser Test eine
Genregulation bei Eukaryoten II
 Genregulation bei Eukaryoten II Aktivierung und Repression der Transkription erfolgen durch Protein-Protein-Wechselwirkungen Protein-Protein-Wechselwirkungen spielen bei der Genregulation der Eukaryoten
Genregulation bei Eukaryoten II Aktivierung und Repression der Transkription erfolgen durch Protein-Protein-Wechselwirkungen Protein-Protein-Wechselwirkungen spielen bei der Genregulation der Eukaryoten
KV: Genexpression und Transkription Michael Altmann
 Institut für Biochemie und Molekulare Medizin KV: Genexpression und Transkription Michael Altmann Herbstsemester 2008/2009 Übersicht VL Genexpression / Transkription 1.) Was ist ein Gen? 2.) Welche Arten
Institut für Biochemie und Molekulare Medizin KV: Genexpression und Transkription Michael Altmann Herbstsemester 2008/2009 Übersicht VL Genexpression / Transkription 1.) Was ist ein Gen? 2.) Welche Arten
GENETIK. für Studierende. Michaela Aubele. für Ahnungslose. Eine Einstiegshilfe. 2. Auflage. Dr. Michaela Aubele, München.
 Michaela Aubele GENETIK für Ahnungslose Eine Einstiegshilfe für Studierende 2. Auflage von Prof. Dr. Michaela Aubele, München Mit 52 Abbildungen und 33 Tabellen S. Hirzel Verlag die VII Vorwort V Kurzer
Michaela Aubele GENETIK für Ahnungslose Eine Einstiegshilfe für Studierende 2. Auflage von Prof. Dr. Michaela Aubele, München Mit 52 Abbildungen und 33 Tabellen S. Hirzel Verlag die VII Vorwort V Kurzer
iphone 4 - Einrichtung des VPN Clients (Cisco VPN Client) / Verbinden des iphones mit einem Exchange
 iphone 4 - Einrichtung des VPN Clients (Cisco VPN Client) / Verbinden des iphones mit einem Exchange Die Verwendung der E-Mail- und Kalenderdienste des Exchange Servers über das iphone kann auf zwei unterschiedlichen
iphone 4 - Einrichtung des VPN Clients (Cisco VPN Client) / Verbinden des iphones mit einem Exchange Die Verwendung der E-Mail- und Kalenderdienste des Exchange Servers über das iphone kann auf zwei unterschiedlichen
Interspergierte Repetitive Elemente
 Interspergierte Repetitive Elemente SINEs = short interspersed nuclear elements LINES = long interspersed nuclear elements MIR = mammalian wide interspersed repeats (Säugerspezifisch?) DNA-Transposons
Interspergierte Repetitive Elemente SINEs = short interspersed nuclear elements LINES = long interspersed nuclear elements MIR = mammalian wide interspersed repeats (Säugerspezifisch?) DNA-Transposons
KV: DNA-Replikation Michael Altmann
 Institut für Biochemie und Molekulare Medizin KV: DNA-Replikation Michael Altmann Herbstsemester 2008/2009 Übersicht VL DNA-Replikation 1.) Das Zentraldogma der Molekularbiologie 1.) Semikonservative Replikation
Institut für Biochemie und Molekulare Medizin KV: DNA-Replikation Michael Altmann Herbstsemester 2008/2009 Übersicht VL DNA-Replikation 1.) Das Zentraldogma der Molekularbiologie 1.) Semikonservative Replikation
Herstellung und Selektion rekombinanter Antikörper
 Herstellung und Selektion rekombinanter Antikörper Für jeden Topf ein Deckel Sintox 16.04.2015 16.04.15 Sintox 1 Inhalte Begriffsklärungen Rekombinant Lymphozyten Antikörper und Antigene Somatische Hypermutation
Herstellung und Selektion rekombinanter Antikörper Für jeden Topf ein Deckel Sintox 16.04.2015 16.04.15 Sintox 1 Inhalte Begriffsklärungen Rekombinant Lymphozyten Antikörper und Antigene Somatische Hypermutation
Lineargleichungssysteme: Additions-/ Subtraktionsverfahren
 Lineargleichungssysteme: Additions-/ Subtraktionsverfahren W. Kippels 22. Februar 2014 Inhaltsverzeichnis 1 Einleitung 2 2 Lineargleichungssysteme zweiten Grades 2 3 Lineargleichungssysteme höheren als
Lineargleichungssysteme: Additions-/ Subtraktionsverfahren W. Kippels 22. Februar 2014 Inhaltsverzeichnis 1 Einleitung 2 2 Lineargleichungssysteme zweiten Grades 2 3 Lineargleichungssysteme höheren als
7. Regulation der Genexpression
 7. Regulation der Genexpression 7.1 Regulation der Enzymaktivität Stoffwechselreaktionen können durch Kontrolle der Aktivität der Enzyme, die diese Reaktionen katalysieren, reguliert werden Feedback-Hemmung
7. Regulation der Genexpression 7.1 Regulation der Enzymaktivität Stoffwechselreaktionen können durch Kontrolle der Aktivität der Enzyme, die diese Reaktionen katalysieren, reguliert werden Feedback-Hemmung
icloud nicht neu, aber doch irgendwie anders
 Kapitel 6 In diesem Kapitel zeigen wir Ihnen, welche Dienste die icloud beim Abgleich von Dateien und Informationen anbietet. Sie lernen icloud Drive kennen, den Fotostream, den icloud-schlüsselbund und
Kapitel 6 In diesem Kapitel zeigen wir Ihnen, welche Dienste die icloud beim Abgleich von Dateien und Informationen anbietet. Sie lernen icloud Drive kennen, den Fotostream, den icloud-schlüsselbund und
Was meinen die Leute eigentlich mit: Grexit?
 Was meinen die Leute eigentlich mit: Grexit? Grexit sind eigentlich 2 Wörter. 1. Griechenland 2. Exit Exit ist ein englisches Wort. Es bedeutet: Ausgang. Aber was haben diese 2 Sachen mit-einander zu tun?
Was meinen die Leute eigentlich mit: Grexit? Grexit sind eigentlich 2 Wörter. 1. Griechenland 2. Exit Exit ist ein englisches Wort. Es bedeutet: Ausgang. Aber was haben diese 2 Sachen mit-einander zu tun?
Primzahlen und RSA-Verschlüsselung
 Primzahlen und RSA-Verschlüsselung Michael Fütterer und Jonathan Zachhuber 1 Einiges zu Primzahlen Ein paar Definitionen: Wir bezeichnen mit Z die Menge der positiven und negativen ganzen Zahlen, also
Primzahlen und RSA-Verschlüsselung Michael Fütterer und Jonathan Zachhuber 1 Einiges zu Primzahlen Ein paar Definitionen: Wir bezeichnen mit Z die Menge der positiven und negativen ganzen Zahlen, also
Statuten in leichter Sprache
 Statuten in leichter Sprache Zweck vom Verein Artikel 1: Zivil-Gesetz-Buch Es gibt einen Verein der selbstbestimmung.ch heisst. Der Verein ist so aufgebaut, wie es im Zivil-Gesetz-Buch steht. Im Zivil-Gesetz-Buch
Statuten in leichter Sprache Zweck vom Verein Artikel 1: Zivil-Gesetz-Buch Es gibt einen Verein der selbstbestimmung.ch heisst. Der Verein ist so aufgebaut, wie es im Zivil-Gesetz-Buch steht. Im Zivil-Gesetz-Buch
Seminar Biochemie. Nukleotide - Nukleinsäuren - Nukleotidstoffwechsel - DNA-Replikation. Dr. Christian Hübbers
 Seminar Biochemie Nukleotide - Nukleinsäuren - Nukleotidstoffwechsel - DNA-Replikation Dr. Christian Hübbers Lernziele Zusammensetzung der Nukleotide (Basen, Zucker) Purin-und Pyrimidinbiosynthese (prinzipieller
Seminar Biochemie Nukleotide - Nukleinsäuren - Nukleotidstoffwechsel - DNA-Replikation Dr. Christian Hübbers Lernziele Zusammensetzung der Nukleotide (Basen, Zucker) Purin-und Pyrimidinbiosynthese (prinzipieller
Was ist Sozial-Raum-Orientierung?
 Was ist Sozial-Raum-Orientierung? Dr. Wolfgang Hinte Universität Duisburg-Essen Institut für Stadt-Entwicklung und Sozial-Raum-Orientierte Arbeit Das ist eine Zusammen-Fassung des Vortrages: Sozialräume
Was ist Sozial-Raum-Orientierung? Dr. Wolfgang Hinte Universität Duisburg-Essen Institut für Stadt-Entwicklung und Sozial-Raum-Orientierte Arbeit Das ist eine Zusammen-Fassung des Vortrages: Sozialräume
Molekulargenetik Biologie am Inhaltsverzeichnis Die Begriffe DNA, Nukleotid, Gen, Chromosom und Epigenom definieren...
 Molekulargenetik Inhaltsverzeichnis Die Begriffe DNA, Nukleotid, Gen, Chromosom und Epigenom definieren... 2 Beschreiben, wie die DNA aufgebaut ist... 3 Den Ablauf der Replikation erklären und dabei die
Molekulargenetik Inhaltsverzeichnis Die Begriffe DNA, Nukleotid, Gen, Chromosom und Epigenom definieren... 2 Beschreiben, wie die DNA aufgebaut ist... 3 Den Ablauf der Replikation erklären und dabei die
40-Tage-Wunder- Kurs. Umarme, was Du nicht ändern kannst.
 40-Tage-Wunder- Kurs Umarme, was Du nicht ändern kannst. Das sagt Wikipedia: Als Wunder (griechisch thauma) gilt umgangssprachlich ein Ereignis, dessen Zustandekommen man sich nicht erklären kann, so dass
40-Tage-Wunder- Kurs Umarme, was Du nicht ändern kannst. Das sagt Wikipedia: Als Wunder (griechisch thauma) gilt umgangssprachlich ein Ereignis, dessen Zustandekommen man sich nicht erklären kann, so dass
