V4 Analyse von Genomsequenzen
|
|
|
- Frank Thomas
- vor 6 Jahren
- Abrufe
Transkript
1 V4 nalyse von enomsequenzen - ene identifizieren Intrinsische und Extrinsische Verfahren: Homologie bzw. Hidden Markov Modelle - ranskriptionsfaktorbindestellen identifizieren Position Specific Scoring Matrices (PSSM) - anz kurz: finde Repeat-Sequenzen Suche nach bekannten Repeat-Motiven - Mapping von NS-Daten auf Referenzgenom - lignment zweier enom-sequenzen Suffix Bäume 1
2 Identifikation von enen Die einfachste Methode, DN Sequenzen zu finden, die für Proteine kodieren, ist nach offenen Leserahmen (open reading frames oder ORFs) zu suchen. In jeder Sequenz gibt es 6 mögliche offene Leserahmen: 3 ORFs starten an den Positionen 1, 2, und 3 und gehen in die 5 3 Richtung, 3 ORFs starten an den Positionen 1, 2, und 3 und gehen in die 5 3 Richtung des komplementären Strangs. In prokaryotischen enomen werden Protein-kodierende DN-Sequenzen gewöhnlich in mrn transkribiert und die mrn wird ohne wesentliche Änderungen direkt in einen minosäurestrang übersetzt. Daher ist der längste ORF von dem ersten verfügbaren Met codon (U) auf der mrn, das als odon für den ranskriptionsstart fungiert, bis zu dem nächsten Stopcodon in demselben offenen Leserahmen, gewöhnlich eine gute Vorhersage für die Protein-kodierende Region. 2
3 Vorhersage von enen in enomsequenzen Etwa die Hälfte aller ene kann durch Homologie zu anderen bekannten enen oder Proteinen gefunden werden ( extrinsische Methode ). Dieser nteil wächst stetig, da die nzahl an sequenzierten enomen und bekannten cdn/es Sequenzen kontinuierlich wächst. Um die übrige Hälfte an enen zu finden, muss man Vorhersage-Methoden einsetzen ( intrinsische Methoden ), die an einem oldstandard-datensatz mit bekannten enen trainiert wurden. 3
4 Hidden Markov Modell (HMM) Ein Hidden Markov Modell ist ein raph, der verschiedene Zustände verbindet. Im Modell rechts gibt es 3 verborgene Zustände: X1, X2, X3. In unserem Fall sind dies Bereiche der DN, z.b. Intron, Promoter, Exon. Zwischen den Zuständen X1 und X2 und zurück und von X2 nach X3 sind hier Übergänge erlaubt. Die Übergangswahrscheinlichkeiten hierfür sind a12, a21 und 23. y1 bis y4 sind die möglichen (sichtbaren) Output-Zustände. Im Fall der en-vorhersage also die Beobachtung, ob die entsprechenden DN- bschnitte als mrn-sequenzen exprimiert werden oder nicht. Die Output-Zustände werden aus den verborgenen Zuständen mit den Wahrscheinlichkeiten b11 bis b34 erzeugt. 4
5 Hidden Markov Modell (HMM) Die opologie des raphen gibt an, zwischen welchen Zuständen Übergänge erlaubt sind. Diese gibt man bei der Spezifikation des HMM vor. Jeder Übergang hängt nur von den beiden Zuständen i und j ab, zwischen denen der Übergang stattfindet, nicht von früheren Zuständen. (Diese Eigenschaft gilt allgemein für Markov-Modelle) Die Übergangswahrscheinlichkeiten aij und bij müssen in der rainingsphase des HMM hergeleitet werden. Ein HMM besteht also aus der opologie und den trainierten Wahrscheinlichkeiten. 5
6 Wettervorhersage mit Hidden Markov Modell Ein efangener im Kerkerverlies möchte das aktuelle Wetter herausfinden. Er weiß, dass auf einen sonnigen ag zu 70 % ein Regentag folgt und dass auf einen Regentag zu 50 % ein Sonnentag folgt. Verborgener Zustand Beobachtung Weiß er zusätzlich, dass die Schuhe der Wärter bei Regen zu 90 % dreckig, bei sonnigem Wetter aber nur zu 60 % dreckig sind, so kann er durch Beobachtung der Wärterschuhe Rückschlüsse über das Wetter ziehen. 6
7 enerkennung mit Hidden Markov Modellen Bei der enerkennung möchte man bestimmen, wo in einem enom Exons (E) und Introns (I) sind. Der Output sind die bekannten exprimierten Sequenzen. us dieser soll jedem Basenpaar der günstigste verborgene Zustand (E/I) zugeordnet werden. Bei Markov-Modelle hängt der Zustand des i-ten Buchstaben nur von seinem direkten Vorgänger, dem (i -1)- ten Buchstaben ab. 7
8 Vergleich von envorhersage-methoden Ein Beispiel, in dem Exonomy die ene richtig erkennt. Ein Beispiel, in dem limmerm die ene richtig erkennt. Ein Beispiel, in dem Unveil die ene richtig erkennt (auch enscan). Majoros et al. Nucl. cids. Res. 31, 3601 (2003) 8
9 Promotervorhersage in E.coli Um E.coli Promoter zu analysieren kann man eine Menge von Promotersequenzen bzgl. der Position alignieren, die den bekannten ranskriptionsstart markiert und in den Sequenzen nach konservierten Regionen suchen. E.coli Promotoren enthalten 3 konservierte Sequenzmerkmale - eine etwa 6bp lange Region mit dem Konsensusmotif bei Position eine etwa 6bp lange Region mit dem Konsensusmotif bei Position die Distanz zwischen den beiden Regionen von etwa 17bp ist relativ konstant 9
10 Machbarkeit der Motivsuche mit dem omputer? ranskriptionsfaktorbindestellen (FBS) mit einem omputerprogramm zu identifizieren ist schwierig, da diese aus kurzen, entarteten Sequenzen bestehen, die häufig ebenfalls durch Zufall auftreten. Das Problem lässt sich daher schwer eingrenzen die Länge des gesuchten Motivs vorher nicht bekannt das Motiv braucht zwischen verschiedenen Promotern nicht stark konserviert sein. die Sequenzen, mit denen man nach dem Motiv sucht, brauchen nicht notwendigerweise dem gesamten Promoter entsprechen 10
11 Suche nach gemeinsamen Sequenzmotiven Wird seit der Verfügbarkeit von Microarray en-expressionsdaten eingesetzt. Durch lustern erhält man ruppen von enen mit ähnlichen Expressionsprofilen (z.b. solche, die zur selben Zeit im Zellzyklus aktiviert sind) Hypothese, dass dieses Profil, zumindest teilweise, durch eine ähnliche Struktur der für die transkriptionelle Regulation verantwortlichen cis-regulatorischen Regionen verursacht wird. Suche nach gemeinsamen Motiven in upstream Region des SS dieser ene (z.b bp für Prokaryoten bzw bp für Eukaryoten). 11
12 Motif-Identifizierung Ohler, Niemann rends en 17, 2 (2001) 12
13 Positions-spezifische ewichtsmatrix Populäres Verfahren wenn es eine Liste von enen gibt, die ein F-Bindungsmotiv gemeinsam haben. Bedingung: gute MSs müssen vorhanden sein. lignment-matrix: wie häufig treten die verschiedenen Buchstaben an jeder Position im lignment auf? Hertz, Stormo (1999) Bioinformatics 15,
14 Positions-spezifische ewichtsmatrix Beispiele für Matrizen, die von YRS verwendet werden: 14
15 Datenbank für eukaryotische ranskriptionsfaktoren: RNSF BIOBase / U Braunschweig / BF Relationelle Datenbank 6 Dateien: FOR Wechselwirkung von Fs SIE ihre DN-Bindungsstelle ENE durch welche sie diese Zielgene regulieren ELL wo kommt Faktor in Zelle vor? MRIX F Nukleotid-ewichtungsmatrix LSS Klassifizierungsschema der Fs Wingender et al. (1998) J Mol Biol 284,241 15
16 Datenbank für eukaryotische ranskriptionsfaktoren: RNSF BIOBase / U Braunschweig / BF Matys et al. (2003) Nucl cid Res 31,374 16
17 Identifizierung von Repeats: RepeatMasker RepeatMasker: durchsucht DN Sequenzen auf - eingefügte bschnitte, die bekannten Repeat-Motiven entsprechen (dazu wird eine lange abelle mit bekannten Motiven verwendet) und - auf Regionen geringer Komplexität (z.b. lange bschnitt ). Output: - detaillierte Liste, wo die Repeats in der Sequenz auftauchen und - eine modifizierte Version der Input-Sequenz, in der die Repeats maskiert sind, z.b. durch N s ersetzt sind. Für die Sequenzvergleiche wird eine effiziente Implementation des Smith- Waterman-otoh lgorithmus verwendet. 17
18 Zusammenfassung Es gibt große Datenbanken (z.b. RNSF) mit Informationen über Promoterstellen. Diese Informationen sind experimentell überprüft. Microarray-Daten erlauben es, nach gemeinsamen Motiven von ko-regulierten enen zu suchen. uch möglich: gemeinsame nnotation in der ene Ontology etc. F-Bindungsmotive sind oft überrepräsentiert in der 1000 bp-region upstream. Die klare Funktion dieser Bindungsmotive ist oft unbekannt. llgemein gilt: - relativ wenige Fs regulieren eine große nzahl an enen - es gibt globale und lokale Fs - ene werden üblicherweise durch mehr als einen F reguliert 18
19 Prozessierung von NS-Daten anzgenomsequenzierung = Whole enome Sequencing (WS) nwendung von WS für mikrobielle Isolate Qualitätskontrolle der Sequenzierungs-reads lignment SNP calling enomvisualisierung enomassemblierung Hier wird dies hema nur grob vorgestellt, NS-Prozessierung wird genauer in Vorlesungen von Prof. Keller, Prof. Marschall und Dr. Schulz behandelt. Danksagung für Folien: Mohamed Hamed 19
20 NS Pipeline im Überblick 1. Extraktion der DN aus biologischer Probe 2. enetic enrichment: Manchmal soll nur eine kleine Region des enoms sequenziert werden (einzelne ene bzw. nur die Exons bei Sequenzierung von eukaryot. enomen). Die Extraktion dieser Regionen aus dem enome nennt man nreicherung (enrichment). 3. Vorbereitung der Bibliothek (Library prep): Für viele Sequenziermaschinen muss die DN für die Sequenzierung vorbereitet werden. 4. Die eigentliche Sequenzierung 5. Rohanalyse (primary analysis): lignment / ssemblierung, SNP calling 6. Eigentliche nalyse (secondary analysis): Identifizierung von kausalen SNPs variants, phänotypische haraktisierung (z.b. Virulenzfaktoren) Wir konzentrieren uns auf die Schritte 5 und 6 NS lect, 2014
21 WS Pipeline für bakterielle Phylotypisierung 21
22 Quality (Phred) score Phred Score (Q): Q = - 10 log 10 P P ist eine bschätzung für den Fehler des Base-calling aus den Rohdaten der Sequenzierung. D.h. ein Fehler von 0.1% (10-3 ) ergibt Q = 30. Base Qualitäts-scores nehmen üblicherweise am Ende der reads ab Deshalb werden die reads vor dem lignment-schritts getrimmt, d.h. gekürzt. 22
23 Qualitätskontrolle - FSQ Die Sequenzqualität pro Base ist im linken Beispiel durchgehend sehr hoch (d.h. Q > 30), im rechten Beispiel etwa ab Position 20 aber unzuverlässig. 23
24 Qualitätskontrolle im lignment-schritt uch bei der lignierung mit dem Referenz-enom muss bewertet werden, ob den Reads zweifelsfreie Positionen zugeordnet werden können. lle Reads werden entfernt, deren Mapping-Qualität geringer als 30 ist, d.h. die Fehlerwahrscheinlichkeit, dass der read auf eine andere Region gemappt wird, ist 0.1% und höher. Verteilung der Mapping Qualitätsscores Entfernung von duplizierten reads, da diese die Qualität des SNP-alling beeinflussen. 24
25 Biologie von SNP-Mutationen Verschiedene menschliche enome unterscheiden sich etwa an jeder 1000-ten Base. Die meisten Variationen sind Unterschiede einzelner Basen. Polymorphismus: vererbter Unterschied Somatische Mutation: erworbener Unterschied 341/Images/416px-Dna-SNP_svg.png 25
26 Mögliche ründe für bweichungen in lignments Ein wahrer SNP Experimenteller Fehler Fehler bei Präparierung der Bibliothek oder bei der PR Base calling Fehler während nalyse von Rohdaten Fehler beim lignment oder beim Mapping-Schritt Fehler in der Sequenz des Referenzgenoms ebräuchliche Software ools: Samtools/bcftools atk Varscan Snv-mix Die usgabe des lignments ist im VF Format (Variant all Format) 26
27 Integrative enome Viewer (IV) 27
28 Phylogenetischer Baum aus core-genome SNPs lnput: WS-Sequenzen für verschiedene Staphylococcus aureus Stämme (nas: nasaler Stamm; inv: invasiver Stamm). Schritt 1: identifiziere SNPs im core-genome (eil des S. aureus-enoms, das alle Stämme gemeinsam haben). Schritt 2: konstruiere Verwandschaftsverhältnissen zwischen den Stämmen. usgabe: phylogenetischer Baum ools 5 Figree Seaview homburg_snp-alignment_140131_no_s12-phyml_tree Mon Mar 17 21:43: S225 S5 SeaView N_017340_ref NS_19_t003 INV_6_t504 INV_5_t504 NS_24_t003 NS_17_t504 NS_4_t504 NS_8_t504 INV_14_t504 INV_15_t504 INV_2_t504 INV_7_t504 INV_9_t003 INV_10_t003 NS_40_t INV_11_t003 N NS_30_t003 NS_37_t003 INV_8_t003 NS_23_t003 NS_22_t003 INV_13_t003 NS_36_t003 NS_18_t504 NS_32_t003 NS_25_t003 INV_4_t003 NS_39_t003 Hamed et al. (2015) lade1 t003 lade t504 Other t003 Infection, enetics and Evolution 28
29 Whole enome lignment (W) Wenn die genomische DN-Sequenz eng verwandter Organismen verfügbar wird, kann man ein lignment von zwei enomen konstruieren. lobale enom-lignments machen nur für eng verwandte Organismen Sinn. Im anderen Fall muss man zuerst die genomischen Rearrangements betrachten. Dann kann man die systenischen Regionen (Regionen, in denen en- Reihenfolge des nächsten gemeinsamen Vorfahrens in beiden Spezies konserviert blieb) betrachten und lokale enom-lignments dieser Regionen produzieren. 29
30 Konservierung von Syntenie zwischen Mensch und Maus Ein typisches 510-kb Segment des Maus-hromosoms 12, das mit einem 600-kb Stück des menschlichen hromosom 14 verwandt ist. Blaue Linien: reziprok eindeutige reffer in beiden enomen. Rote Markierungen kennzeichnen die Länge der passenden Regionen. Die bstände zwischen diesen Landmarks sind im Maus-enom kleiner als im Mensch, was mit der 14% kürzeren esamtlänge des enoms übereinstimmt. he mouse genome. Nature 420,
31 Entsprechung syntenischer Regionen 342 Segmente und 217 Blöcke >300 kb mit konservierter Syntenie im Mensch sind im Maus-enom markiert. Jede Farbe entspricht einem bestimmten menschlichen hromosom. he mouse genome. Nature 420,
32 Sensitivität Im globalen Mensch:Maus lignment sind mehr als eine Millionen Regionen stärker als 70% konserviert (auf 100-bp Level) diese Regionen decken > 200 Million bp ab. Nur 62% von ihnen werden von (lokalen) BL-reffern abgedeckt. Dies bedeutet, daß man 38% der konservierten bschnitte nur durch das globale lignment finden kann! Idee: lokales lignment soll als nker-verfahren für anschliessendes globales lignment dienen. Dadurch hofft man, viele zusätzliche konservierte Regionen ausserhalb der nker-regionen zu finden. ouronne,..., Dubchak, enome Res. 13, 73 (2003) 32
33 nkerbasierte Methoden für W Diese Methoden versuchen, sich entsprechende eile der Buchstabenfolgen der betrachteten Sequenzen zu finden, die wahrscheinlich zu einem globalen lignment gehören werden. (Diese teilweisen reffer können durch lokale lignments gefunden werden). Sie bilden nker in den beiden zu alignierenden Sequenzen. In diesen Methoden werden zuerst die nkerpunkte aligniert und dann die Lücken dazwischen geschlossen. MUMmer ist eine sehr erfolgreiche Implementation dieser Strategie für das lignment zweier genomischer Sequenzen. 33
34 Was ist MUMmer?.L. Delcher et al. 1999, 2002 Nucleic cids Res. nimm an, dass zwei Sequenzen eng verwandt sind (sehr ähnlich) MUMmer kann zwei bakterielle enome in weniger als 1 Minute alignieren nutzt Suffix-Bäume um Maximal Unique Matches zu finden Definition eines Maximal Unique Matches (MUM): Eine Subsequenz, die in beiden Sequenzen genau einmal ohne bweichungen vorkommt und in keine Richtung verlängert werden kann. rundidee: ein MUM ausreichender Länge wird sicher eil eines globalen lignments sein. maximal unique matching subsequence (MUM) of 39 nt (shown in uppercase) shared by enome and enome B. ny extension of the MUM will result in a mismatch. By definition, an MUM does not occur anywhere else in either genome. Delcher et al. Nucleic cids Res 27, 2369 (1999) 34
35 MUMmer: wichtige Schritte Erkenne MUMs (Länge wird vom Benutzer festgelegt)
36 Definition von MUMmers Für zwei Strings S1 und S2 und einen Parameter l Der Substring u ist eine MUM Sequenz wenn gilt:! u > l! u kommt genau einmal in S1 und genau einmal in S2 (Eindeutigkeit) vor! Für jeden Buchstaben a kommt weder ua noch au sowohl in S1 als auch in S2 vor (Maximalität) 36
37 Wie findet man MUMs? Naiver nsatz Vergleiche alle eilsequenzen von mit allen eilsequenzen von B. Dies dauert O(n n ) verwende Suffix-Bäume als Datenstruktur ein naiver nsatz, einen Suffix-Baum zu konstruieren hat eine quadratische Komplexität in der Rechenzeit und dem Speicherplatz durch klevere Benutzung von Pointern gibt es lineare lgorithmen in Rechenzeit und Speicherplatz wie den lgorithmus von Mcreight 37
38 Suffix-Bäume Suffix-Bäume sind seit über 30 Jahren wohl etabliert. Einige ihrer Eigenschaften: ein Suffix beginnt an jeder Position I der Sequenz und reicht bis zu ihrem Ende. Eine Sequenz der Länge N hat N Suffices. Es gibt N Blätter. Jeder interne Knoten hat mindest zwei Kinder. 2 Kanten aus dem selben Knoten können nicht mit dem selben Buchstaben beginnen. m Ende wird angefügt 38
39 Konstruktion eines Suffix-Baums Suffixes:
40 Konstruktion eines Suffix-Baums Suffixes:
41 Konstruktion eines Suffix-Baums Suffixes:
42 Konstruktion eines Suffix-Baums Suffixes:
43 Konstruktion eines Suffix-Baums Suffixes:
44 Konstruktion eines Suffix-Baums Suffixes:
45 Konstruktion eines Suffix-Baums Suffixes:
46 Konstruktion eines Suffix-Baums Suffixes:
47 47 Suchen in einem Suffix-Baum Search Pattern:
48 48 Suchen in einem Suffix-Baum Search Pattern:
49 Sortieren der MUMs MUMs werden nach ihren Positionen in enom sortiert enome : enome B: enome : enome B: Jeder MUM ist nur mit seiner Nummer gekennzeichnet, ohne Berücksichtigung seiner Länge. Das obere lignment zeigt alle MUMs. Die Verschiebung von MUM 5 in enom B zeigt eine ransposition an. Die Verschiebung von MUM 3 könnte ein Zufallstreffer oder eil einer inexakten Repeat-Sequenz sein. Unteres lignment: suche in beiden enomen die längste gemeinsam ansteigende Folge an Subsequenzen 49
50 Beispiel: lignment zweier Mikroorganismen Das enom von M.genitalium ist nur etwa 2/3 so lang wie das von M.pneumoniae. Obere bbildung: FS-lignment von M.genitalium und M.pneumoniae. Mitte: lignment mit 25mers Unten: lignment mit MUMs. 5 ranslokationen. Ein Punkt bedeutet jeweils einen reffer zwischen den enomen. FS-Plot: ähnliche ene 25-mer-Plot: 25-Basen-Sequenz, die in beiden Sequenzen genau einmal vorkommt. MUM-Plot: MUM-reffer. Delcher et al. Nucleic cids Res 27, 2369 (1999) 50
51 Beispiel: lignment Mensch:Maus lignment von weiter entfernt liegenden Spezies: Mensch gegen Maus. Hier: lignment einer bp eilsequenz auf dem menschlichen hromosom 12, accession no. U47924, gegen eine bp lange eilsequenz des Mauschromosoms 6. Jeder Punkt des Plots entspricht einem MUM von [ge]15 bp. Delcher et al. Nucleic cids Res 27, 2369 (1999) 51
52 Zusammenfassung Die nwendung der Suffix-Bäume war ein Durchbruch für die lignierung ganzer enome MUMmer 2 besitzt zusätzliche Verbesserung für die Rechenzeit und den Speicherplatz die Verwendung von Suffix-rrays anstatt von Suffix-Bäumen gibt eine verbesserte Datenstruktur ( Stefan Kurtz, Hamburg) es wird nun möglich, mehr als zwei enome zu alignieren (implementiert in M) 52
V4 Analyse von Genomsequenzen
 V4 nalyse von enomsequenzen - ene identifizieren Intrinsische und Extrinsische Verfahren: Homologie bzw. Hidden Markov Modelle - ranskriptionsfaktorbindestellen identifizieren Position Specific Scoring
V4 nalyse von enomsequenzen - ene identifizieren Intrinsische und Extrinsische Verfahren: Homologie bzw. Hidden Markov Modelle - ranskriptionsfaktorbindestellen identifizieren Position Specific Scoring
V4 Analyse von Genomsequenzen
 V4 nalyse von enomsequenzen - ene identifizieren Intrinsische und Extrinsische Verfahren: Homologie bzw. Hidden Markov Modelle - ranskriptionsfaktorbindestellen identifizieren Position Specific Scoring
V4 nalyse von enomsequenzen - ene identifizieren Intrinsische und Extrinsische Verfahren: Homologie bzw. Hidden Markov Modelle - ranskriptionsfaktorbindestellen identifizieren Position Specific Scoring
Algorithmen und Datenstrukturen in der Bioinformatik Zweites Übungsblatt WS 05/06 Musterlösung
 Johanna Ploog, Konstantin Clemens Freie Universität Berlin Institut für Mathematik II Arbeitsgruppe für Mathematik in den Lebenswissenschaften Algorithmen und Datenstrukturen in der Bioinformatik Zweites
Johanna Ploog, Konstantin Clemens Freie Universität Berlin Institut für Mathematik II Arbeitsgruppe für Mathematik in den Lebenswissenschaften Algorithmen und Datenstrukturen in der Bioinformatik Zweites
Bioinformatik. Lokale Alignierung Gapkosten. Silke Trißl / Ulf Leser Wissensmanagement in der. Bioinformatik
 Bioinformatik Lokale Alignierung Gapkosten Silke Trißl / Ulf Leser Wissensmanagement in der Bioinformatik Inhalt dieser Vorlesung Ähnlichkeit Lokales und globales Alignment Gapped Alignment Silke Trißl:
Bioinformatik Lokale Alignierung Gapkosten Silke Trißl / Ulf Leser Wissensmanagement in der Bioinformatik Inhalt dieser Vorlesung Ähnlichkeit Lokales und globales Alignment Gapped Alignment Silke Trißl:
MBI: Sequenz-Vergleich mit Alignment
 MBI: Sequenz-Vergleich mit Alignment Bernhard Haubold 28. Oktober 2014 Wiederholung: Was ist Bioinformatik? Historische Übersicht; CABIOS Bioinformatics Gemeinsames Thema: Information in vivo DNA Epigenetik
MBI: Sequenz-Vergleich mit Alignment Bernhard Haubold 28. Oktober 2014 Wiederholung: Was ist Bioinformatik? Historische Übersicht; CABIOS Bioinformatics Gemeinsames Thema: Information in vivo DNA Epigenetik
Multiple Alignments. Vorlesung Einführung in die Angewandte Bioinformatik Prof. Dr. Sven Rahmann. Webseite zur Vorlesung
 Multiple Alignments Vorlesung Einführung in die Angewandte Bioinformatik Prof. Dr. Sven Rahmann Webseite zur Vorlesung http://bioinfo.wikidot.com/ Sprechstunde Mo 16-17 in OH14, R214 Sven.Rahmann -at-
Multiple Alignments Vorlesung Einführung in die Angewandte Bioinformatik Prof. Dr. Sven Rahmann Webseite zur Vorlesung http://bioinfo.wikidot.com/ Sprechstunde Mo 16-17 in OH14, R214 Sven.Rahmann -at-
Algorithmen für paarweise Sequenz-Alignments. Katharina Hembach
 Proseminar Bioinformatik WS 2010/11 Algorithmen für paarweise Sequenz-Alignments Katharina Hembach 06.12.2010 1 Einleitung Paarweise Sequenz-Alignments spielen in der Bioinformatik eine wichtige Rolle.
Proseminar Bioinformatik WS 2010/11 Algorithmen für paarweise Sequenz-Alignments Katharina Hembach 06.12.2010 1 Einleitung Paarweise Sequenz-Alignments spielen in der Bioinformatik eine wichtige Rolle.
Gleichheit, Ähnlichkeit, Homologie
 Gleichheit, Ähnlichkeit, Homologie Identität (identity) Verhältnis der Anzahl identischer Aminosäuren zur Gesamtzahl der Aminosäuren; objektiv Ähnlichkeit (similarity) Verhältnis ähnlicher Aminosäuren
Gleichheit, Ähnlichkeit, Homologie Identität (identity) Verhältnis der Anzahl identischer Aminosäuren zur Gesamtzahl der Aminosäuren; objektiv Ähnlichkeit (similarity) Verhältnis ähnlicher Aminosäuren
Bayesianische Netzwerke - Lernen und Inferenz
 Bayesianische Netzwerke - Lernen und Inferenz Manuela Hummel 9. Mai 2003 Gliederung 1. Allgemeines 2. Bayesianische Netzwerke zur Auswertung von Genexpressionsdaten 3. Automatische Modellselektion 4. Beispiel
Bayesianische Netzwerke - Lernen und Inferenz Manuela Hummel 9. Mai 2003 Gliederung 1. Allgemeines 2. Bayesianische Netzwerke zur Auswertung von Genexpressionsdaten 3. Automatische Modellselektion 4. Beispiel
Masterarbeit. Variantentolerantes Readmapping durch Locality Sensitive Hashing. Jens Quedenfeld November Gutachter: Sven Rahmann Dominik Köppl
 Masterarbeit Variantentolerantes Readmapping durch Locality Sensitive Hashing Jens Quedenfeld November 2015 Gutachter: Sven Rahmann Dominik Köppl Technische Universität Dortmund Fakultät für Informatik
Masterarbeit Variantentolerantes Readmapping durch Locality Sensitive Hashing Jens Quedenfeld November 2015 Gutachter: Sven Rahmann Dominik Köppl Technische Universität Dortmund Fakultät für Informatik
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
Übungsaufgaben zur Einführung in die Bioinformatik - Lösungen
 18.01.2013 Prof. P. Güntert 1 Vorlesung BPC I: Aspekte der Thermodynamik in der Strukturbiologie Übungsaufgaben zur Einführung in die Bioinformatik - Lösungen 1. Hamming und Levenshtein Distanzen a) Was
18.01.2013 Prof. P. Güntert 1 Vorlesung BPC I: Aspekte der Thermodynamik in der Strukturbiologie Übungsaufgaben zur Einführung in die Bioinformatik - Lösungen 1. Hamming und Levenshtein Distanzen a) Was
AlgoBio WS 16/17 Protein-DNA Interaktionen ChiP-Seq Datenanalyse. Annalisa Marsico
 AlgoBio WS 16/17 Protein-DNA Interaktionen ChiP-Seq Datenanalyse Annalisa Marsico 6.02.2017 Protein-DNA Interaktionen Häufig binden sich Proteine an DNA, um ihre biologische Funktion zu regulieren. Transkriptionsfaktoren
AlgoBio WS 16/17 Protein-DNA Interaktionen ChiP-Seq Datenanalyse Annalisa Marsico 6.02.2017 Protein-DNA Interaktionen Häufig binden sich Proteine an DNA, um ihre biologische Funktion zu regulieren. Transkriptionsfaktoren
Algorithmen auf Sequenzen
 Algorithmen auf Sequenzen Vorlesung von Prof. Dr. Sven Rahmann im Sommersemester 2008 Kapitel 6 Alignments Webseite zur Vorlesung http://ls11-www.cs.tu-dortmund.de/people/rahmann/teaching/ss2008/algorithmenaufsequenzen
Algorithmen auf Sequenzen Vorlesung von Prof. Dr. Sven Rahmann im Sommersemester 2008 Kapitel 6 Alignments Webseite zur Vorlesung http://ls11-www.cs.tu-dortmund.de/people/rahmann/teaching/ss2008/algorithmenaufsequenzen
BCDS - Biochemische Datenbanken und Software
 BCDS - Biochemische Datenbanken und Software Seminarinhalte Bioinformatische Genom- und Proteomanalyse Literaturrecherche und Zitation Naturwissenschaftliche Software Termine 25. Mai, 1. Juni, 8. Juni,
BCDS - Biochemische Datenbanken und Software Seminarinhalte Bioinformatische Genom- und Proteomanalyse Literaturrecherche und Zitation Naturwissenschaftliche Software Termine 25. Mai, 1. Juni, 8. Juni,
Zentrum für Bioinformatik. Übung 4: Revision. Beispielfragen zur Klausur im Modul Angewandte Bioinformatik (erste Semesterhälfte)
 Andrew Torda Björn Hansen Iryna Bondarenko Zentrum für Bioinformatik Übung zur Vorlesung Angewandte Bioinformatik Sommersemester 2014 20./23.06.2014 Übung 4: Revision Beispielfragen zur Klausur im Modul
Andrew Torda Björn Hansen Iryna Bondarenko Zentrum für Bioinformatik Übung zur Vorlesung Angewandte Bioinformatik Sommersemester 2014 20./23.06.2014 Übung 4: Revision Beispielfragen zur Klausur im Modul
Bioinformatik Für Biophysiker
 Bioinformatik Für Biophysiker Sommersemester 2009 Silke Trißl / Ulf Leser Wissensmanagement in der Bioinformatik Wissensmanagement in der Bioinformatik Schwerpunkte Algorithmen der Bioinformatik Management
Bioinformatik Für Biophysiker Sommersemester 2009 Silke Trißl / Ulf Leser Wissensmanagement in der Bioinformatik Wissensmanagement in der Bioinformatik Schwerpunkte Algorithmen der Bioinformatik Management
Zusammenfassung des 2. Abends
 lgorithmen in der iologie r. Hans-Joachim öckenhauer r. ennis Komm Zusammenfassung des. bends Zürich, 0. pril 0 lignment-verfahren Für einen Überblick über die lignment-lgorithmen zur estimmung der Ähnlichkeit
lgorithmen in der iologie r. Hans-Joachim öckenhauer r. ennis Komm Zusammenfassung des. bends Zürich, 0. pril 0 lignment-verfahren Für einen Überblick über die lignment-lgorithmen zur estimmung der Ähnlichkeit
Bioinformatik für Lebenswissenschaftler
 Bioinformatik für Lebenswissenschaftler Oliver Kohlbacher, Steffen Schmidt SS 2010 11. Hiden Markov Models & Phylogenien Abt. Simulation biologischer Systeme WSI/ZBIT, Eberhard Karls Universität Tübingen
Bioinformatik für Lebenswissenschaftler Oliver Kohlbacher, Steffen Schmidt SS 2010 11. Hiden Markov Models & Phylogenien Abt. Simulation biologischer Systeme WSI/ZBIT, Eberhard Karls Universität Tübingen
Bioinformatik für Lebenswissenschaftler
 Bioinformatik für Lebenswissenschaftler Oliver Kohlbacher, Steffen Schmidt SS 2010 11. Hiden Markov Models & Phylogenien Abt. Simulation biologischer Systeme WSI/ZBIT, Eberhard Karls Universität Tübingen
Bioinformatik für Lebenswissenschaftler Oliver Kohlbacher, Steffen Schmidt SS 2010 11. Hiden Markov Models & Phylogenien Abt. Simulation biologischer Systeme WSI/ZBIT, Eberhard Karls Universität Tübingen
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 3. Aus welchen vier Nukleotiden ist RNA aufgebaut? 4. DNA RNA 5. Ein Wissenschaftler
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 3. Aus welchen vier Nukleotiden ist RNA aufgebaut? 4. DNA RNA 5. Ein Wissenschaftler
Grundlagen der Bioinformatik
 rundlagen der Bioinformatik Vergleich von DN - Sequenzen Ulf Leser Wissensmanagement in der Bioinformatik Ulf Leser: Proseminar Bioinformatik, SoSe 2008 3 Was ist ein en? C C C C Chromosom DN C C C RN
rundlagen der Bioinformatik Vergleich von DN - Sequenzen Ulf Leser Wissensmanagement in der Bioinformatik Ulf Leser: Proseminar Bioinformatik, SoSe 2008 3 Was ist ein en? C C C C Chromosom DN C C C RN
Algorithmische Bioinformatik
 lgorithmische Bioinformatik Stringalignment Ulf Leser Wissensmanagement in der Bioinformatik Inhalt dieser Vorlesung pproximative Stringvergleiche Dotplots Edit-bstand und lignment Naiver lgorithmus Ulf
lgorithmische Bioinformatik Stringalignment Ulf Leser Wissensmanagement in der Bioinformatik Inhalt dieser Vorlesung pproximative Stringvergleiche Dotplots Edit-bstand und lignment Naiver lgorithmus Ulf
4.9.7 Konstruktion der Suffixbäume
 .9.7 Konstruktion der Suffixbäume Beipiel: xabxa (siehe Abbildung.27) Man beginnt mit der Konstruktion eines Suffixbaumes für gesamten String und schreibt eine 1 am Blatt, weil der Suffix xabxa an der
.9.7 Konstruktion der Suffixbäume Beipiel: xabxa (siehe Abbildung.27) Man beginnt mit der Konstruktion eines Suffixbaumes für gesamten String und schreibt eine 1 am Blatt, weil der Suffix xabxa an der
Anwendungen von HMM. Kapitel 1 Spezialvorlesung Modul (Fortgeschrittene Methoden in der Bioinformatik) Jana Hertel
 Anwendungen von HMM Kapitel 1 Spezialvorlesung Modul 10-202-2206 (Fortgeschrittene Methoden in der Bioinformatik) Jana Hertel Professur für Bioinformatik Institut für Informatik Universität Leipzig Machine
Anwendungen von HMM Kapitel 1 Spezialvorlesung Modul 10-202-2206 (Fortgeschrittene Methoden in der Bioinformatik) Jana Hertel Professur für Bioinformatik Institut für Informatik Universität Leipzig Machine
Prüfung Molekulare Genetik
 Prüfung Molekulare enetik SBH06 Name: Maximale Punktzahl: 40 Erreichte Punktzahl: Note: Seite 1 von 7 ufgabe 1 Wie bezeichnet man den Vorgang der Übersetzung von RN in Proteine? Translation Transformation
Prüfung Molekulare enetik SBH06 Name: Maximale Punktzahl: 40 Erreichte Punktzahl: Note: Seite 1 von 7 ufgabe 1 Wie bezeichnet man den Vorgang der Übersetzung von RN in Proteine? Translation Transformation
IR Seminar SoSe 2012 Martin Leinberger
 IR Seminar SoSe 2012 Martin Leinberger Suchmaschinen stellen Ergebnisse häppchenweise dar Google: 10 Ergebnisse auf der ersten Seite Mehr Ergebnisse gibt es nur auf Nachfrage Nutzer geht selten auf zweite
IR Seminar SoSe 2012 Martin Leinberger Suchmaschinen stellen Ergebnisse häppchenweise dar Google: 10 Ergebnisse auf der ersten Seite Mehr Ergebnisse gibt es nur auf Nachfrage Nutzer geht selten auf zweite
B*-BÄUME. Ein Index ist seinerseits wieder nichts anderes als eine Datei mit unpinned Records.
 B*-Bäume 1 B*-BÄUME Beobachtung: Ein Index ist seinerseits wieder nichts anderes als eine Datei mit unpinned Records. Es gibt keinen Grund, warum man nicht einen Index über einem Index haben sollte, und
B*-Bäume 1 B*-BÄUME Beobachtung: Ein Index ist seinerseits wieder nichts anderes als eine Datei mit unpinned Records. Es gibt keinen Grund, warum man nicht einen Index über einem Index haben sollte, und
TU München. Hauptseminar: WS 2002 / Einführung in Suffix - Bäume
 TU München Hauptseminar: WS 2002 / 2003 Einführung in Suffix - Bäume Bearbeiterin: Shasha Meng Betreuerin: Barbara König Inhalt 1. Einleitung 1.1 Motivation 1.2 Eine kurze Geschichte 2. Tries 2.1 Basisdefinition
TU München Hauptseminar: WS 2002 / 2003 Einführung in Suffix - Bäume Bearbeiterin: Shasha Meng Betreuerin: Barbara König Inhalt 1. Einleitung 1.1 Motivation 1.2 Eine kurze Geschichte 2. Tries 2.1 Basisdefinition
Algorithmen und Anwendungen zur Kartierung von Genomen
 Algorithmen und Anwendungen zur Kartierung von Genomen Dr. Dominik Grimm Probelehrveranstaltung Wissenschaftszentrum Straubing Hochschule Weihenstephan-Triesdorf Straubing, 14. Juli 2017 14. Juli 2017
Algorithmen und Anwendungen zur Kartierung von Genomen Dr. Dominik Grimm Probelehrveranstaltung Wissenschaftszentrum Straubing Hochschule Weihenstephan-Triesdorf Straubing, 14. Juli 2017 14. Juli 2017
Von der DNA zur Datenbank: Sequenzierung & Assemblierung
 Vorlesung Einführung in die Bioinforma4k SoSe 2012 Von der DN zur Datenbank: Sequenzierung & ssemblierung Prof. Daniel Huson ZBI enter for Bioinformatics Entdeckung der DN Friedrich Miescher (1844-1895)
Vorlesung Einführung in die Bioinforma4k SoSe 2012 Von der DN zur Datenbank: Sequenzierung & ssemblierung Prof. Daniel Huson ZBI enter for Bioinformatics Entdeckung der DN Friedrich Miescher (1844-1895)
Algorithmen und Datenstrukturen II
 Algorithmen und Datenstrukturen II Algorithmen zur Textverarbeitung III: D. Rösner Institut für Wissens- und Sprachverarbeitung Fakultät für Informatik Otto-von-Guericke Universität Magdeburg Sommer 2009,
Algorithmen und Datenstrukturen II Algorithmen zur Textverarbeitung III: D. Rösner Institut für Wissens- und Sprachverarbeitung Fakultät für Informatik Otto-von-Guericke Universität Magdeburg Sommer 2009,
5 Sequenz-/Strukturalignments
 5 Sequenz-/Strukturalignments Modul 10-202-2208 Bioinformatik von RN- und Proteinstrukturen Jana Hertel Lehrstuhl Bioinformatik 29. pril 2013 Jana Hertel (Lehrstuhl Bioinformatik) 5 Sequenz-/Strukturalignments
5 Sequenz-/Strukturalignments Modul 10-202-2208 Bioinformatik von RN- und Proteinstrukturen Jana Hertel Lehrstuhl Bioinformatik 29. pril 2013 Jana Hertel (Lehrstuhl Bioinformatik) 5 Sequenz-/Strukturalignments
Informatik II, SS 2018
 Informatik II - SS 2018 (Algorithmen & Datenstrukturen) Vorlesung 4 (30.4.2018) Sortieren IV Algorithmen und Komplexität Analyse Merge Sort Laufzeit T(n) setzt sich zusammen aus: Divide und Merge: O n
Informatik II - SS 2018 (Algorithmen & Datenstrukturen) Vorlesung 4 (30.4.2018) Sortieren IV Algorithmen und Komplexität Analyse Merge Sort Laufzeit T(n) setzt sich zusammen aus: Divide und Merge: O n
Biochemisches Grundpraktikum
 Biochemisches Grundpraktikum Dr. Ellen Hornung; Email: ehornun@gwdg.de; Tel: 39-5748 Einteilung der Praktikumsplätze: Eintragen in Listen am - Dienstag, 10.11.2009, von 12:00 13:00 - Freitag, 13.11.2009,
Biochemisches Grundpraktikum Dr. Ellen Hornung; Email: ehornun@gwdg.de; Tel: 39-5748 Einteilung der Praktikumsplätze: Eintragen in Listen am - Dienstag, 10.11.2009, von 12:00 13:00 - Freitag, 13.11.2009,
Algorithmische Bioinformatik
 Algorithmische Bioinformatik Gene Finding mit Markov-Modellen Ulf Leser Wissensmanagement in der Bioinformatik Ziel der Vorlesung Einstieg in statistische Verfahren Problemstellung Statistisches Patternmatching
Algorithmische Bioinformatik Gene Finding mit Markov-Modellen Ulf Leser Wissensmanagement in der Bioinformatik Ziel der Vorlesung Einstieg in statistische Verfahren Problemstellung Statistisches Patternmatching
Algorithmische Anwendungen WS 2005/2006
 Algorithmische Anwendungen WS 2005/2006 Sequenzalignment Gruppe F_lila_Ala0506 Allal Kharaz Yassine ELassad Inhaltsverzeichnis 1 Problemstellungen...................................... 3 1.1 Rechtschreibkorrektur...............................
Algorithmische Anwendungen WS 2005/2006 Sequenzalignment Gruppe F_lila_Ala0506 Allal Kharaz Yassine ELassad Inhaltsverzeichnis 1 Problemstellungen...................................... 3 1.1 Rechtschreibkorrektur...............................
2. Woche Eindeutige Entschlüsselbarleit, Sätze von Kraft und McMillan, Huffmancodierung
 2 Woche Eindeutige Entschlüsselbarleit, Sätze von Kraft und McMillan, Huffmancodierung 2 Woche: Eindeutige Entschlüsselbarleit, Sätze von Kraft und McMillan, Huffmancodierung 24/ 44 Zwei Beispiele a 0
2 Woche Eindeutige Entschlüsselbarleit, Sätze von Kraft und McMillan, Huffmancodierung 2 Woche: Eindeutige Entschlüsselbarleit, Sätze von Kraft und McMillan, Huffmancodierung 24/ 44 Zwei Beispiele a 0
AlgoBio WS 16/17 Differenzielle Genexpression. Annalisa Marsico
 AlgoBio WS 16/17 Differenzielle Genexpression Annalisa Marsico 04.01.2017 Pipeline für die Mikroarray-Analyse Bildanalyse Hintergrundkorrektur Normalisierung Vorverarbeitung Zusammenfassung Quantifizierung
AlgoBio WS 16/17 Differenzielle Genexpression Annalisa Marsico 04.01.2017 Pipeline für die Mikroarray-Analyse Bildanalyse Hintergrundkorrektur Normalisierung Vorverarbeitung Zusammenfassung Quantifizierung
FOLDALIGN und sein Algorithmus. Nadine Boley Silke Szymczak
 FOLDALIGN und sein Algorithmus Nadine Boley Silke Szymczak Gliederung 2 Einleitung Motivation des Ansatzes zu FOLDALIGN Sankoff-Algorithmus Globales Alignment Zuker-Algorithmus Kombination FOLDALIGN Algorithmus,
FOLDALIGN und sein Algorithmus Nadine Boley Silke Szymczak Gliederung 2 Einleitung Motivation des Ansatzes zu FOLDALIGN Sankoff-Algorithmus Globales Alignment Zuker-Algorithmus Kombination FOLDALIGN Algorithmus,
Sequenzanalyse mit Markov-Ketten
 Sequenzanalyse mit Markov-Ketten Andreas Spillner Bioinformatik, SS 208 Ausgangspunkt Die Abfolge von Buchstaben in einer Sequenz ist zufällig, aber es gibt in der Regel Abhängigkeiten zwischen benachbarten
Sequenzanalyse mit Markov-Ketten Andreas Spillner Bioinformatik, SS 208 Ausgangspunkt Die Abfolge von Buchstaben in einer Sequenz ist zufällig, aber es gibt in der Regel Abhängigkeiten zwischen benachbarten
Hämophilie Symposium, März , Reitter Sylvia
 Hämophilie Symposium, März 2010 FVIII-Gen liegt auf Xq28 (langer Arm des X-Chromosoms) x Hämophilie Erbgang I Hämophilie Erbgang II FVIII-Gen besteht aus 26 Exons mit 186 Kilobasenpaaren (kb); Exon 14
Hämophilie Symposium, März 2010 FVIII-Gen liegt auf Xq28 (langer Arm des X-Chromosoms) x Hämophilie Erbgang I Hämophilie Erbgang II FVIII-Gen besteht aus 26 Exons mit 186 Kilobasenpaaren (kb); Exon 14
Projektgruppe. Text Labeling mit Sequenzmodellen
 Projektgruppe Enes Yigitbas Text Labeling mit Sequenzmodellen 4. Juni 2010 Motivation Möglichkeit der effizienten Verarbeitung von riesigen Datenmengen In vielen Bereichen erwünschte automatisierte Aufgabe:
Projektgruppe Enes Yigitbas Text Labeling mit Sequenzmodellen 4. Juni 2010 Motivation Möglichkeit der effizienten Verarbeitung von riesigen Datenmengen In vielen Bereichen erwünschte automatisierte Aufgabe:
Informationsvisualisierung
 Informationsvisualisierung Thema: 7. Visualisierung Biologischer Daten Dozent: Dr. Dirk Zeckzer zeckzer@informatik.uni-leipzig.de Sprechstunde: nach Vereinbarung Umfang: 2 Prüfungsfach: Modul Fortgeschrittene
Informationsvisualisierung Thema: 7. Visualisierung Biologischer Daten Dozent: Dr. Dirk Zeckzer zeckzer@informatik.uni-leipzig.de Sprechstunde: nach Vereinbarung Umfang: 2 Prüfungsfach: Modul Fortgeschrittene
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr
 Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
MBI: Sequenzvergleich ohne Alignment
 MBI: Sequenzvergleich ohne Alignment Bernhard Haubold 12. November 2013 Wiederholung Exaktes & inexaktes Matching Das exakte Matching Problem Naive Lösung Präprozessierung Muster(Pattern): Z-Algorithmus,
MBI: Sequenzvergleich ohne Alignment Bernhard Haubold 12. November 2013 Wiederholung Exaktes & inexaktes Matching Das exakte Matching Problem Naive Lösung Präprozessierung Muster(Pattern): Z-Algorithmus,
Informationsgehalt von DNA
 Informationsgehalt von DNA Topics Genes code, gene organisation, signals, gene detection Genomes genome organisation, nucleotide patterns, junk DNA DNA als Informationsträger DNA Building Blocks Desoxyribose
Informationsgehalt von DNA Topics Genes code, gene organisation, signals, gene detection Genomes genome organisation, nucleotide patterns, junk DNA DNA als Informationsträger DNA Building Blocks Desoxyribose
Algorithmen und Datenstrukturen in der Bioinformatik Drittes Übungsblatt WS 05/06 Musterlösung
 Konstantin Clemens Johanna Ploog Freie Universität Berlin Institut für Mathematik II Arbeitsgruppe für Mathematik in den Lebenswissenschaften Algorithmen und Datenstrukturen in der Bioinformatik Drittes
Konstantin Clemens Johanna Ploog Freie Universität Berlin Institut für Mathematik II Arbeitsgruppe für Mathematik in den Lebenswissenschaften Algorithmen und Datenstrukturen in der Bioinformatik Drittes
Informatik II, SS 2018
 Informatik II - SS 2018 (Algorithmen & Datenstrukturen) Vorlesung 21 (11.7.2018) String Matching (Textsuche) II Greedy Algorithmen I Algorithmen und Komplexität Textsuche / String Matching Gegeben: Zwei
Informatik II - SS 2018 (Algorithmen & Datenstrukturen) Vorlesung 21 (11.7.2018) String Matching (Textsuche) II Greedy Algorithmen I Algorithmen und Komplexität Textsuche / String Matching Gegeben: Zwei
Bioinformatik Für Biophysiker
 Bioinformatik Für Biophysiker Wintersemester 2005 / 2006 Ulf Leser Wissensmanagement in der Bioinformatik Wissensmanagement in der Bioinformatik Lehrstuhl seit 10/2002 Schwerpunkte Algorithmen der Bioinformatik
Bioinformatik Für Biophysiker Wintersemester 2005 / 2006 Ulf Leser Wissensmanagement in der Bioinformatik Wissensmanagement in der Bioinformatik Lehrstuhl seit 10/2002 Schwerpunkte Algorithmen der Bioinformatik
Algorithmische Bioinformatik
 Algorithmische Bioinformatik Suffixbäume Ulf Leser Wissensmanagement in der Bioinformatik Ziele Perspektivenwechsel: Von Online zu Offline-Stringmatching Verständnis von Suffix-Bäumen als Datenstruktur
Algorithmische Bioinformatik Suffixbäume Ulf Leser Wissensmanagement in der Bioinformatik Ziele Perspektivenwechsel: Von Online zu Offline-Stringmatching Verständnis von Suffix-Bäumen als Datenstruktur
KV: Genexpression und Transkription Michael Altmann
 Institut für Biochemie und Molekulare Medizin KV: Genexpression und Transkription Michael Altmann Herbstsemester 2008/2009 Übersicht VL Genexpression / Transkription 1.) Was ist ein Gen? 2.) Welche Arten
Institut für Biochemie und Molekulare Medizin KV: Genexpression und Transkription Michael Altmann Herbstsemester 2008/2009 Übersicht VL Genexpression / Transkription 1.) Was ist ein Gen? 2.) Welche Arten
Pairwise Alignment. Steffen Forkmann. Proseminar: BioInformatik
 Pairwise Alignment Steffen Forkmann Proseminar: BioInformatik Wintersemester 2004/2005 Inhaltsverzeichnis 1 Problemstellungen 3 1.1 Rechtschreibkorrektur............................... 3 1.2 DNA- und Aminosäure-Sequenzen........................
Pairwise Alignment Steffen Forkmann Proseminar: BioInformatik Wintersemester 2004/2005 Inhaltsverzeichnis 1 Problemstellungen 3 1.1 Rechtschreibkorrektur............................... 3 1.2 DNA- und Aminosäure-Sequenzen........................
Informatik II, SS 2014
 Informatik II SS 2014 (Algorithmen & Datenstrukturen) Vorlesung 4 (7.5.2014) Asymptotische Analyse, Sortieren IV Algorithmen und Komplexität Erfahrungen 1. Übung C++ / Java sind komplett ungewohnt Struktur
Informatik II SS 2014 (Algorithmen & Datenstrukturen) Vorlesung 4 (7.5.2014) Asymptotische Analyse, Sortieren IV Algorithmen und Komplexität Erfahrungen 1. Übung C++ / Java sind komplett ungewohnt Struktur
Vorlesung Datenstrukturen
 Vorlesung Datenstrukturen Graphdurchläufe Maike Buchin 22. und 27.6.2017 Graphexploration Motivation: Für viele Zwecke will man den gesamten Graphen durchlaufen, zb. um festzustellen ob er (stark) zusammenhängt.
Vorlesung Datenstrukturen Graphdurchläufe Maike Buchin 22. und 27.6.2017 Graphexploration Motivation: Für viele Zwecke will man den gesamten Graphen durchlaufen, zb. um festzustellen ob er (stark) zusammenhängt.
ADS: Algorithmen und Datenstrukturen 1
 ADS: Algorithmen und Datenstrukturen 1 Teil 15: Fragestunde Uwe Quasthoff Institut für Informatik Abteilung Automatische Sprachverarbeitung Universität Leipzig 30. Januar 2018 [Letzte Aktualisierung: 30/01/2018,
ADS: Algorithmen und Datenstrukturen 1 Teil 15: Fragestunde Uwe Quasthoff Institut für Informatik Abteilung Automatische Sprachverarbeitung Universität Leipzig 30. Januar 2018 [Letzte Aktualisierung: 30/01/2018,
Konstruktion von Suffix Bäumen
 Konstruktion von Suffix Bäumen Prof. Dr. S. Albers Prof. Dr. Th. Ottmann 1 Ukkonen s Algorithmus: Impliziter Suffix Baum Definition: Ein impliziter Suffix Baum ist der Baum, den man aus dem Suffix Baum
Konstruktion von Suffix Bäumen Prof. Dr. S. Albers Prof. Dr. Th. Ottmann 1 Ukkonen s Algorithmus: Impliziter Suffix Baum Definition: Ein impliziter Suffix Baum ist der Baum, den man aus dem Suffix Baum
Bayesianische Netzwerke I
 Bayesianische Netzwerke I Christiane Belitz 2.5.2003 Überblick Der Vortrag basiert auf Using Bayesian Networks to Analyze Expression Data von Friedman et al. (2000) Definition: Bayesianisches Netzwerk
Bayesianische Netzwerke I Christiane Belitz 2.5.2003 Überblick Der Vortrag basiert auf Using Bayesian Networks to Analyze Expression Data von Friedman et al. (2000) Definition: Bayesianisches Netzwerk
Quadratische Gleichungen
 Einführung und Begriffe Gleichungen, in denen die Unbekannte in der zweiten Potenz vorkommt, heissen quadratische Gleichungen oder Gleichungen zweiten Grades. Beispiele: 4, t 3t, y y y 4, 5z 3z 1 z 4,
Einführung und Begriffe Gleichungen, in denen die Unbekannte in der zweiten Potenz vorkommt, heissen quadratische Gleichungen oder Gleichungen zweiten Grades. Beispiele: 4, t 3t, y y y 4, 5z 3z 1 z 4,
Vorlesung Informatik 2 Algorithmen und Datenstrukturen. (25 Sortieren vorsortierter Daten)
 Vorlesung Informatik 2 Algorithmen und Datenstrukturen (25 Sortieren vorsortierter Daten) 1 Untere Schranke für allgemeine Sortierverfahren Satz Zum Sortieren einer Folge von n Schlüsseln mit einem allgemeinen
Vorlesung Informatik 2 Algorithmen und Datenstrukturen (25 Sortieren vorsortierter Daten) 1 Untere Schranke für allgemeine Sortierverfahren Satz Zum Sortieren einer Folge von n Schlüsseln mit einem allgemeinen
Sequence Assembly. Nicola Palandt
 Sequence Assembly Nicola Palandt 1 Einleitung Das Genom eines Lebewesens ist der Träger aller Informationen, die eine Zelle weitergeben kann. Es besteht aus Sequenzen, die mehrere Milliarden Basen lang
Sequence Assembly Nicola Palandt 1 Einleitung Das Genom eines Lebewesens ist der Träger aller Informationen, die eine Zelle weitergeben kann. Es besteht aus Sequenzen, die mehrere Milliarden Basen lang
Alignment-Verfahren zum Vergleich biologischer Sequenzen
 zum Vergleich biologischer Sequenzen Hans-Joachim Böckenhauer Dennis Komm Volkshochschule Zürich. April Ein biologisches Problem Fragestellung Finde eine Methode zum Vergleich von DNA-Molekülen oder Proteinen
zum Vergleich biologischer Sequenzen Hans-Joachim Böckenhauer Dennis Komm Volkshochschule Zürich. April Ein biologisches Problem Fragestellung Finde eine Methode zum Vergleich von DNA-Molekülen oder Proteinen
Kapitel 7: Sequenzen- Alignierung in der Bioinformatik
 Kapitel 7: Sequenzen- Alignierung in der Bioinformatik VO Algorithm Engineering Professor Dr. Petra Mutzel Lehrstuhl für Algorithm Engineering, LS11 19. VO 14. Juni 2007 1 Literatur für diese VO Volker
Kapitel 7: Sequenzen- Alignierung in der Bioinformatik VO Algorithm Engineering Professor Dr. Petra Mutzel Lehrstuhl für Algorithm Engineering, LS11 19. VO 14. Juni 2007 1 Literatur für diese VO Volker
Kapitel 3: Sortierverfahren Gliederung
 Gliederung 1. Grundlagen 2. Zahlentheoretische Algorithmen 3. Sortierverfahren 4. Ausgewählte Datenstrukturen 5. Dynamisches Programmieren 6. Graphalgorithmen 7. String-Matching 8. Kombinatorische Algorithmen
Gliederung 1. Grundlagen 2. Zahlentheoretische Algorithmen 3. Sortierverfahren 4. Ausgewählte Datenstrukturen 5. Dynamisches Programmieren 6. Graphalgorithmen 7. String-Matching 8. Kombinatorische Algorithmen
5.4 Hierarchische Verfahren
 Ziel Grundlagen Konstruktion einer Hierarchie von lustern (meist repräsentiert durch ein sog. Dendrogramm), ) so dass immer die luster mit minimaler i Distanz verschmolzen werden Dendrogramm ein Baum,
Ziel Grundlagen Konstruktion einer Hierarchie von lustern (meist repräsentiert durch ein sog. Dendrogramm), ) so dass immer die luster mit minimaler i Distanz verschmolzen werden Dendrogramm ein Baum,
Übung 1 Bioinformatik. Ihre Namen:
 Evolutionsbiologie 2 Übung 1 Bioinformatik WS2018/2019 Ihre Namen: llgemeine Hinweise: Für die Zulassung zur Klausur muss dieses Übungsblatt bearbeitet und als bestanden bewertet sein. Sie können das Übungsblatt
Evolutionsbiologie 2 Übung 1 Bioinformatik WS2018/2019 Ihre Namen: llgemeine Hinweise: Für die Zulassung zur Klausur muss dieses Übungsblatt bearbeitet und als bestanden bewertet sein. Sie können das Übungsblatt
C SB. Genomics Herausforderungen und Chancen. Genomics. Genomic data. Prinzipien dominieren über Detail-Fluten. in 10 Minuten!
 Genomics Herausforderungen und Chancen Prinzipien dominieren über Detail-Fluten Genomics in 10 Minuten! biol. Prin cip les Genomic data Dr.Thomas WERNER Scientific & Business Consulting +49 89 81889252
Genomics Herausforderungen und Chancen Prinzipien dominieren über Detail-Fluten Genomics in 10 Minuten! biol. Prin cip les Genomic data Dr.Thomas WERNER Scientific & Business Consulting +49 89 81889252
7. Variabilität. Die Variabilität
 Die Variabilität DIA 48 Variabilität Zwischen Mitgliedern der Populationen gibt es phänotypische Unterschiede. Mit Ausnahme der eineiigen Zwillinge gibt es keine identischen Individuen. Die phänotypische
Die Variabilität DIA 48 Variabilität Zwischen Mitgliedern der Populationen gibt es phänotypische Unterschiede. Mit Ausnahme der eineiigen Zwillinge gibt es keine identischen Individuen. Die phänotypische
Informatik II, SS 2014
 Informatik II SS 2014 (Algorithmen & Datenstrukturen) Vorlesung 20 (23.7.2014) All Pairs Shortest Paths, String Matching (Textsuche) Algorithmen und Komplexität Vorlesungsevaluation Sie sollten alle eine
Informatik II SS 2014 (Algorithmen & Datenstrukturen) Vorlesung 20 (23.7.2014) All Pairs Shortest Paths, String Matching (Textsuche) Algorithmen und Komplexität Vorlesungsevaluation Sie sollten alle eine
Informatik II, SS 2016
 Informatik II - SS 2016 (Algorithmen & Datenstrukturen) Vorlesung 10 (27.5.2016) Binäre Suchbäume II Algorithmen und Komplexität Zusätzliche Dictionary Operationen Dictionary: Zusätzliche mögliche Operationen:
Informatik II - SS 2016 (Algorithmen & Datenstrukturen) Vorlesung 10 (27.5.2016) Binäre Suchbäume II Algorithmen und Komplexität Zusätzliche Dictionary Operationen Dictionary: Zusätzliche mögliche Operationen:
Einführung in die Bioinformatik
 Einführung in die Bioinformatik Ringvorlesung Biologie Sommer 07 Burkhard Morgenstern Institut für Mikrobiologie und Genetik Abteilung für Bioinformatik Goldschmidtstr. 1 Online Materialien zur Ringvorlesung:
Einführung in die Bioinformatik Ringvorlesung Biologie Sommer 07 Burkhard Morgenstern Institut für Mikrobiologie und Genetik Abteilung für Bioinformatik Goldschmidtstr. 1 Online Materialien zur Ringvorlesung:
8.4 Suffixbäume. Anwendungen: Information Retrieval, Bioinformatik (Suche in Sequenzen) Veranschaulichung: DNA-Sequenzen
 8.4 Suffixbäume Ziel: Datenstruktur, die effiziente Operationen auf (langen) Zeichenketten unterstützt: - Suche Teilzeichenkette (Substring) - Präfix - längste sich wiederholende Zeichenkette -... Anwendungen:
8.4 Suffixbäume Ziel: Datenstruktur, die effiziente Operationen auf (langen) Zeichenketten unterstützt: - Suche Teilzeichenkette (Substring) - Präfix - längste sich wiederholende Zeichenkette -... Anwendungen:
Pharmazeutische Biologie WS2011/2012. Das neue Paradigma: Personalisierte Medizin
 2. Vorlesung Pharmazeutische Biologie WS2011/2012 Das neue Paradigma: Personalisierte Medizin Prof. Theo Dingermann Institut für Pharmazeutische Biologie Biozentrum Max-von Laue-Str. 9 60438 Frankfurt
2. Vorlesung Pharmazeutische Biologie WS2011/2012 Das neue Paradigma: Personalisierte Medizin Prof. Theo Dingermann Institut für Pharmazeutische Biologie Biozentrum Max-von Laue-Str. 9 60438 Frankfurt
Kaninchen: 1 cagattgaggagagcaccaccatcgtcacctcgcagttggcggaggtcagcgcagccgag 60
 Ergebnisse 6 3. Ergebnisse 3. Charakterisierung der zelllinienspezifischen cdn Die Entwicklung zweier Zelllinien, des epithelialen Trophoblasten und des pluripotenten Embryoblasten, ist der erste Differenzierungsschritt
Ergebnisse 6 3. Ergebnisse 3. Charakterisierung der zelllinienspezifischen cdn Die Entwicklung zweier Zelllinien, des epithelialen Trophoblasten und des pluripotenten Embryoblasten, ist der erste Differenzierungsschritt
Kapitel 7: Optimalcodierung und Huffman Coding
 Kapitel 7: codierung und Huffman Coding Ziele des Kapitels Auftreten von Fehlern bei zu starker Kompression Konstruktion optimaler Codes Huffman Coding 2 Bisher Theorem (Shannon I): Die mittlere Codewortlänge
Kapitel 7: codierung und Huffman Coding Ziele des Kapitels Auftreten von Fehlern bei zu starker Kompression Konstruktion optimaler Codes Huffman Coding 2 Bisher Theorem (Shannon I): Die mittlere Codewortlänge
Personalisierte Medizin
 Personalisierte Medizin Möglichkeiten und Grenzen Prof. Dr. Friedemann Horn Universität Leipzig, Institut für Klinische Immunologie, Molekulare Immunologie Fraunhofer Institut für Zelltherapie und Immunologie
Personalisierte Medizin Möglichkeiten und Grenzen Prof. Dr. Friedemann Horn Universität Leipzig, Institut für Klinische Immunologie, Molekulare Immunologie Fraunhofer Institut für Zelltherapie und Immunologie
Zwei zentrale Fragen...
 Zwei zentrale Fragen... Wie können schädliche Mutation in Sequenzdaten aufgespürt werden? Wie kann überprüft werden ob eine Mutation schädlich/kausal ist? 2 Die Referenzsequenz (= der genetische Bauplan
Zwei zentrale Fragen... Wie können schädliche Mutation in Sequenzdaten aufgespürt werden? Wie kann überprüft werden ob eine Mutation schädlich/kausal ist? 2 Die Referenzsequenz (= der genetische Bauplan
Andrej Aderhold Problemseminar Thema. Gaidatzis, Nimwegen, Hausser, Zavolan, March2007, BMC
 Andrej Aderhold Problemseminar Thema Inference of mirna targets using evolutionary conservation and pathway analysis Gaidatzis, Nimwegen, Hausser, Zavolan, March2007, BMC Bioinformatics Übersicht mirna
Andrej Aderhold Problemseminar Thema Inference of mirna targets using evolutionary conservation and pathway analysis Gaidatzis, Nimwegen, Hausser, Zavolan, March2007, BMC Bioinformatics Übersicht mirna
Datenstrukturen und Algorithmen. 7. Suchen in linearen Feldern
 Datenstrukturen und Algorithmen 7. Suchen in linearen Feldern VO 708.031 Suchen in linearen Feldern robert.legenstein@igi.tugraz.at 1 Inhalt der Vorlesung 1. Motivation, Einführung, Grundlagen 2. Algorithmische
Datenstrukturen und Algorithmen 7. Suchen in linearen Feldern VO 708.031 Suchen in linearen Feldern robert.legenstein@igi.tugraz.at 1 Inhalt der Vorlesung 1. Motivation, Einführung, Grundlagen 2. Algorithmische
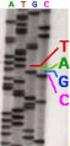
4.1 Restriktionsenzymverdau von PCR-Produkten des β-catenin-gens
 4 Ergebnisse 4.1 Restriktionsenzymverdau von PR-Produkten des β-atenin-ens Für die Mutationsanalyse im Exon 3 des β-atenin-ens wurde in 19 Fällen die genomische DN aus umorgewebe untersucht, indem wie
4 Ergebnisse 4.1 Restriktionsenzymverdau von PR-Produkten des β-atenin-ens Für die Mutationsanalyse im Exon 3 des β-atenin-ens wurde in 19 Fällen die genomische DN aus umorgewebe untersucht, indem wie
Bioinformatik Für Biophysiker
 Bioinformatik Für Biophysiker Wintersemester 2006 / 2007 Ulf Leser Wissensmanagement in der Bioinformatik Wissensmanagement in der Bioinformatik Lehrstuhl seit 10/2002 Schwerpunkte Algorithmen der Bioinformatik
Bioinformatik Für Biophysiker Wintersemester 2006 / 2007 Ulf Leser Wissensmanagement in der Bioinformatik Wissensmanagement in der Bioinformatik Lehrstuhl seit 10/2002 Schwerpunkte Algorithmen der Bioinformatik
Pharmazeutische Biologie WS2011/2012. Das neue Paradigma: Personalisierte Medizin
 3. Vorlesung Pharmazeutische Biologie WS2011/2012 Das neue Paradigma: Personalisierte Medizin Prof. Theo Dingermann Institut für Pharmazeutische Biologie Biozentrum Max-von Laue-Str. 9 60438 Frankfurt
3. Vorlesung Pharmazeutische Biologie WS2011/2012 Das neue Paradigma: Personalisierte Medizin Prof. Theo Dingermann Institut für Pharmazeutische Biologie Biozentrum Max-von Laue-Str. 9 60438 Frankfurt
Praktikum Algorithmischen Anwendungen WS 2006/07 Bioinformatik Sequence-Aligment Team C rot Ala0607
 Praktikum Algorithmischen Anwendungen WS 2006/07 Bioinformatik Sequence-Aligment Team C rot Ala0607 Blöink, Frank 11038619 ai600@gm.fh-koeln.de Wolters, Benjamin 11037092 ai651@gm.fh-koeln.de 26. Januar
Praktikum Algorithmischen Anwendungen WS 2006/07 Bioinformatik Sequence-Aligment Team C rot Ala0607 Blöink, Frank 11038619 ai600@gm.fh-koeln.de Wolters, Benjamin 11037092 ai651@gm.fh-koeln.de 26. Januar
Transkription Teil 2. - Transkription bei Eukaryoten -
 Transkription Teil 2 - Transkription bei Eukaryoten - Inhalte: Unterschiede in der Transkription von Pro- und Eukaryoten Die RNA-Polymerasen der Eukaryoten Cis- und trans-aktive Elemente Promotoren Transkriptionsfaktoren
Transkription Teil 2 - Transkription bei Eukaryoten - Inhalte: Unterschiede in der Transkription von Pro- und Eukaryoten Die RNA-Polymerasen der Eukaryoten Cis- und trans-aktive Elemente Promotoren Transkriptionsfaktoren
Übung II. Einführung, Teil 1. Arbeiten mit Ensembl
 Übung II Einführung, Teil 1 Arbeiten mit Ensembl Ensembl Genome Browser (Bereitstellung von Vielzeller Genomen) Projekt wurde 1999 initiiert Projektpartner EMBL European Bioinformatics Institute (EBI)
Übung II Einführung, Teil 1 Arbeiten mit Ensembl Ensembl Genome Browser (Bereitstellung von Vielzeller Genomen) Projekt wurde 1999 initiiert Projektpartner EMBL European Bioinformatics Institute (EBI)
Organisation und Evolution des Genoms
 Organisation und Evolution des Genoms Organisation und Evolution des Genoms Definition Genom: vollständige DNA-Sequenz eines Organismus I. Einfachstes Genom: Prokaryoten Zwei Gruppen, evolutionär unterschiedlicher
Organisation und Evolution des Genoms Organisation und Evolution des Genoms Definition Genom: vollständige DNA-Sequenz eines Organismus I. Einfachstes Genom: Prokaryoten Zwei Gruppen, evolutionär unterschiedlicher
Ausprägungsfach Bioinformatik im Rahmen des Bachelor-Studiengangs Informatik. CIBIV Center for Integrative Bioinformatics Vienna
 Ausprägungsfach Bioinformatik im Rahmen des Bachelor-Studiengangs Informatik Center for Integrative Bioinformatics Vienna (CIBIV) Max F. Perutz Laboratories (MFPL) Vienna, Austria http://www.cibiv.at CIBIV
Ausprägungsfach Bioinformatik im Rahmen des Bachelor-Studiengangs Informatik Center for Integrative Bioinformatics Vienna (CIBIV) Max F. Perutz Laboratories (MFPL) Vienna, Austria http://www.cibiv.at CIBIV
Algorithmische Bioinformatik
 lgorithmische Bioinformatik pproximatives Stringmatching Edit-bstand Ulf Leser Wissensmanagement in der Bioinformatik Ziele dieser Vorlesung Einstieg in exaktes approximatives Stringmatching Bedeutung
lgorithmische Bioinformatik pproximatives Stringmatching Edit-bstand Ulf Leser Wissensmanagement in der Bioinformatik Ziele dieser Vorlesung Einstieg in exaktes approximatives Stringmatching Bedeutung
Vorlesungsthemen Mikrobiologie
 Vorlesungsthemen Mikrobiologie 1. Einführung in die Mikrobiologie B. Bukau 2. Zellaufbau von Prokaryoten B. Bukau 3. Bakterielles Wachstum und Differenzierung B. Bukau 4. Bakterielle Genetik und Evolution
Vorlesungsthemen Mikrobiologie 1. Einführung in die Mikrobiologie B. Bukau 2. Zellaufbau von Prokaryoten B. Bukau 3. Bakterielles Wachstum und Differenzierung B. Bukau 4. Bakterielle Genetik und Evolution
Algorithmen und Datenstrukturen
 Algorithmen und Datenstrukturen Prof. Martin Lercher Institut für Informatik Heinrich-Heine-Universität Düsseldorf Teil 10 Suche in Graphen Version vom 13. Dezember 2016 1 / 2 Vorlesung 2016 / 2017 2 /
Algorithmen und Datenstrukturen Prof. Martin Lercher Institut für Informatik Heinrich-Heine-Universität Düsseldorf Teil 10 Suche in Graphen Version vom 13. Dezember 2016 1 / 2 Vorlesung 2016 / 2017 2 /
Einführung in die Bioinformatik
 Einführung in die Bioinformatik SS 2013 1. Was ist Bioinformatik? Kay Nieselt Integrative Transkriptomik Zentrum für Bioinformatik Tübingen Kay.Nieselt@uni-tuebingen.de Ablauf und Formales Ringvorlesung
Einführung in die Bioinformatik SS 2013 1. Was ist Bioinformatik? Kay Nieselt Integrative Transkriptomik Zentrum für Bioinformatik Tübingen Kay.Nieselt@uni-tuebingen.de Ablauf und Formales Ringvorlesung
Komplexität von Algorithmen:
 Komplexität von Algorithmen: Ansatz: Beschreiben/erfassen der Komplexität über eine Funktion, zur Abschätzung des Rechenaufwandes abhängig von der Größe der Eingabe n Uns interessiert: (1) Wie sieht eine
Komplexität von Algorithmen: Ansatz: Beschreiben/erfassen der Komplexität über eine Funktion, zur Abschätzung des Rechenaufwandes abhängig von der Größe der Eingabe n Uns interessiert: (1) Wie sieht eine
Programm heute. Algorithmen und Datenstrukturen (für ET/IT) Entartete Suchbäume. Beispiel: Balancieren von Suchbaum. Wintersemester 2012/13
 Programm heute Algorithmen und Datenstrukturen (für ET/IT) Wintersemester / Fortgeschrittene Datenstrukturen Dr. Tobias Lasser Computer Aided Medical Procedures Technische Universität München 8 Such-Algorithmen
Programm heute Algorithmen und Datenstrukturen (für ET/IT) Wintersemester / Fortgeschrittene Datenstrukturen Dr. Tobias Lasser Computer Aided Medical Procedures Technische Universität München 8 Such-Algorithmen
Bioinformatik. Approximatives Stringmatching Editabstand. Ulf Leser Wissensmanagement in der. Bioinformatik
 Bioinformatik pproximatives Stringmatching Editabstand Ulf Leser Wissensmanagement in der Bioinformatik Naiver nsatz 1. P und an Position 1 ausrichten 2. Vergleiche P mit von links nach rechts Zwei ungleiche
Bioinformatik pproximatives Stringmatching Editabstand Ulf Leser Wissensmanagement in der Bioinformatik Naiver nsatz 1. P und an Position 1 ausrichten 2. Vergleiche P mit von links nach rechts Zwei ungleiche
Bioinformatik. BLAST Basic Local Alignment Search Tool. Ulf Leser Wissensmanagement in der. Bioinformatik
 Bioinformatik BLAST Basic Local Alignment Search Tool Ulf Leser Wissensmanagement in der Bioinformatik Heuristische Alignierung Annotation neuer Sequenzen basiert auf Suche nach homologen Sequenzen in
Bioinformatik BLAST Basic Local Alignment Search Tool Ulf Leser Wissensmanagement in der Bioinformatik Heuristische Alignierung Annotation neuer Sequenzen basiert auf Suche nach homologen Sequenzen in
BLAST. Datenbanksuche mit BLAST. Genomische Datenanalyse 10. Kapitel
 Datenbanksuche mit BLAST BLAST Genomische Datenanalyse 10. Kapitel http://www.ncbi.nlm.nih.gov/blast/ Statistische Fragen Datenbanksuche Query Kann die globale Sequenzähnlichkeit eine Zufallsfluktuation
Datenbanksuche mit BLAST BLAST Genomische Datenanalyse 10. Kapitel http://www.ncbi.nlm.nih.gov/blast/ Statistische Fragen Datenbanksuche Query Kann die globale Sequenzähnlichkeit eine Zufallsfluktuation
