2. Seminar:
|
|
|
- Jörg Peters
- vor 5 Jahren
- Abrufe
Transkript
1 2. Seminar: Ballaset al. (1993): Identification of the Auxin-responsive Element, AuxRE, in the Primary indoleacetic Acid-inducible Gene, PS- IAA4/5, of Pea (Pisumsativum). J Mol Biol 233: Ulmasovet al. (1997): ARF1, a transcription factor that binds to auxin response elements. Science 276:
2 preliminary model (1993) Ub AXR1? Ub E3 E2 Ub repressor? Ub Ub Ub Ub AXR1similar to ubiquitin-activating enzyme E1 auxin response
3 Hintergründe bis dahin bekannt (1993): schnelle Induktion der Zellelongation durch Auxin (~15-25 min) transkriptionelleinduktion verschiedener Gene geht der phys. Reaktion voraus. Hypothese: Auxin reguliert Zellelongation über Veränderung von Genexpressionsmustern Auxin-responsiveGene wurden in Erbse, Sojabohne und Arabidopsisidentifiziert, die untereinander eine sehr hohe Homologie aufweisen und Kriterien als primäre Auxinresponsegene erfüllen: Induktion der Expression schnell und spezifisch durch Auxin Induktion erfordert keine de novo Proteinbiosynthese erforderliche Signalelemente liegen bereits vor
4 1. paper Ziel: Identifizierung der Promotorsequenz, die für die Auxin responsein Auxin-induzierbaren Genen verantwortlich ist = Auxin Response Element (AuxRE) = Versuchen den Signalweg vom Ende her zu entschlüsseln (erst die Promotorsequenz, dann Transkriptionsfaktoren, Interaktionsproteine der Transkriptionsfaktoren...) 4
5 Voraussetzung: Etablierung eines Auxin-induzierbaren Protoplastensystems / Reportersystems Lokalisation des AuxREerfordert das Testen vieler verschiedener (chimärer) Konstrukte stabile Trafo(sehr aufwändig+ zeitintensiv + funktioniert nicht mit jeder Pflanzenart gleich gut) transiente Transfektionmit Protoplasten (leichter zugänglich für die Aufnahme von DNA-Konstruktenund Chemikalien als komplexe Gewebe) NotwendigerTest: Überprüfen ob sich die Protoplasten genauso verhalten wie intakte Keimlinge (Auxin response)
6 test protoplasts vs. epicotyls Kontrolle IAA 2,4-D NAA GA ABA BA IAA4/5 IAA4/5 IAA6 pwi1 pwi1 + IAA Kontrolle 20 µm IAA 6 Protoplasten Epicotyle
7 test protoplasts vs. epicotyls IAA4/5 Kontrolle IAA 2,4-D NAA GA ABA BA IAA4/5Induktionin Protoplasten IAA6 IAA4/5 pwi1 gleicht der in Epicotylen wird spezifisch durch Auxine induziert erfolgt schnell, pwi1 Transkriptmengeakkumuliert + IAA in Abhäng. Kontrolle der Behandlungsdauer µm IAA Protoplasten Epicotyle 7
8 Konz. abhängigkeit IAA4/5 pwi1 IAA4/5 Expression nimm mit steigener Auxinkonz. zu Inhibierungder Proteinbiosynthese aktiviert Expression auch in Abwesenheit von Auxin! 1. Signalelemente müssen nicht erst gebildet werden 2. fehlende Aktivierung im Grundzustand vermutlich durch Repressorproteine 8
9 Konz. abhängigkeit IAA4/5 pwi1 Auxin responsein Protoplasten ist mit der von Epicotylen vergleichbar kann für weitere Experimente genutzt werden IAA4/5 Expression nimm mit steigener Auxinkonz. zu Inhibierungder Proteinbiosynthese aktiviert Expression auch in Abwesenheit von Auxin! 1. Signalelemente müssen nicht erst gebildet werden 2. fehlende Aktivierung im Grundzustand vermutlich durch Repressorproteine 9
10 Transkriptionelle Fusion (chimäre Konstrukte) Promotor XY Gen XY GFP Promotor XY + Reportergen Luciferase ß-Glucuronidase(GUS) CAT Aktivierung Promotor XY Reportergen Nachweis der mrna Nachweis der Proteinaktivität
11 Transkriptionelle Fusion (chimäre Konstrukte) Promotor XY Gen XY GFP Promotor XY + Reportergen Luciferase ß-Glucuronidase(GUS) CAT Aktivierung Promotor XY Reportergen Nachweis der mrna Nachweis der Proteinaktivität
12 CAT reporter system CAT = Chloramphenicol acetyltransferase Enzym kann das Antibiotikum Chloramphenicolneutralisieren, indem Acetylgruppen übertragen werden -CAT + CAT 12
13 CAT reportersystem Test des CAT reporter systems K kein Promotor konstitutiver Promotor IAA4/5 Promotor IAA4/5::CAT: CAT-Aktivität spiegelt die Auxin responsedes Promotors zeit-und konzentrationsabhängig wider 13
14 AufklärungderPromotorstruktur primer extension: i.d.r. ersterschritt zur Charakterisierung von Promotorbereichen/Erhalt vollständiger Transkripte Identifizierungdes Transkriptionsstarts (TATAbox, 5 UTR) TATA? ATG Promotor? 5 UTR? reverse Transkription IAA4/5 IAA4/5 (mrna) P 32 Primer 14
15 Primer extension IAA4/5 (mrna) P 32 Primer 3 Transkriptionsstarts identifiziert: 93, 95 und 99 bpvor dem Start ATG Experiment wurde auch mit Primer Extension aus dem chimärenkonstrukt (IAA4/5:CAT) wiederholt = gleiches Ergebnis ACGT Pr Epi 15
16 promoter deletion analysis basale CATAktivität vermindert -aber Auxin response funktioniert noch keine/kaum CATAktivität CAT Aktivität Vom 5 Ende her markiert Position -318 die Grenze zur Position des AuxRE 16
17 promoter deletion analysis markiert 3 Endedes AuxRE
18 promoter deletion analysis Das AuxREliegt im Bereich von -154 bis
19 Testender core sequence min.promotor = keine CAT Aktivität AuxRE= Auxin-induzierter Anstieg der CAT Aktivität inv.auxre= geringe Induktion der CAT Aktivität min.promotor = kaum CAT Aktivität AuxRE= Auxin-induzierter Anstieg der CAT Aktivität inv.auxre= geringe Induktion der CAT Aktivität (-318 AuxRE-154) reicht für die Auxin response aus korrekte Orientierung ist essentiel! 19
20 in vivo reporter assay Konstrukte in Tabak transformiert GUS IAA4/5 Promotor GUS -318 IAA4/5 Prom. GUS Bestätigung der Region -318 bis -154 als notwendig für die Auxin response + Faktoren die dafür in Erbse nötig sind finden sich auch in Tabak -188 IAA4/5 GUS 20
21 Bereichwurdeauf 164 bp eingegrenzt(-318 bis-154) DNaseI footprinting Liegen Bindestellen für kernlokalisierte Proteine (Transkriptionsfaktoren) in diesem Bereich? DNase I footprinting 21
22 Nr. 3 / 10 Nr. 4 / 5 / 6 (-IAA) Nr. 7 / 8 / 9 (+IAA) - IAA + IAA 22
23 - IAA komplementärer Strang - IAA + IAA 23
24 - IAA komplementärer Strang - IAA + IAA 24
25 Strukturdes AuxRE II-VI: five sequence motifs identified by Oeller et al. (1993) footprint C/E CACATGCTCATGTTTC palindrome sequence TGTCCCAT (1993) found in: auxin-responsive genes of P. sativum, soybean and A. thaliana 25
26 Modelle(1993) 26
27 1. paper Fazit: Es konnten zwei verschiedene Sequenzbereiche identifiziert werden, die zusammen die Auxin response vermitteln. Für beide Bereiche konnte die Bindung von Kernproteinen gezeigt werden + konservierte Sequenzen gefunden werden die in Auxin-responsivenGenen verschiedener Arten auftreten 27
28 2.paper Science (1997) Ziel: weitere Charakterisierung des AuxRE Identifizierung von Proteinen, die mit AuxRE interagieren Hintergrund: AuxREwurde anhand eines anderen Promotors (GH3aus Sojabohne) als konservierte Sequenz TGTCTC identifiziert Motif weist Homologie zu Glucocorticoid Motif(TGTTCT) auf, das i.d.r als Palindromsequenz(AGAACAnnnTGTTCT) vorliegt liegen AuxRE auch in Palindromen vor? 28
29 quantitativergus assay fluorimetrische Quantifizierung der Blaufärbung Test in Möhren Protoplasten D0: eins der zwei AuxRE des GH3 Promotors 29
30 Yeast-one-hybridsystem Identifizierung von Proteinen, die an das AuxRE binden können 1. cdnaexpressionlibrary(jeweiliges Protein wird mit einer Aktivierungsdomäne verbunden) 2. AuxRE wird mit einem LacZ reporter verbunden bindet ein Protein (aus der cdnaexpressionlibrary) anddas AuxRE, kommt es zur Aktivierung der LacZExpression und die entsprechenden Hefezellen werden je nach Reportergen blau oder können auf einem Minimalmedium wachsen auf dem ohne Expression des Reporters kein Wachstum möglich ist. 30
31 Yeast-one-hybrid screen 5 cdna Klone wurden identifiziert alle kodieren für das gleiche Protein: ARF1 Sequenzhomologie zu VP1(TF aus Mais) und ABI1(Homologes Gen in Arabidopsis) mögliche NLS Sequenzhomologie zu AUX/IAAs (putative TFs) 31
32 StrukturderGene 32
33 alignments 33
34 gel mobility shift assay Nachweis der Bindung eines Proteins an DNA DNA Fragmente an die ein Protein gebunden vorliegt, bewegen sich langsamer im Gel als freie DNA Stücke (abhängig von der Größe und Anzahl der gebundenen Proteine). 34
35 gel mobility shift assay C ARF1 Deletionen N ARF1wird von AuxRE gebunden Deletionendie in die VP1homologe Region reichen (C286bzw. N63und N154) können kein P3(2x) mehr binden = DNA Bindedomäne liegt am N-terminus 35
36 quantitativergus assay Welche Basen im Motif sind essentiell für die Auxininduktion? + GUS Protoplasten keine Auxininduktion der GUS Aktivität 36
37 DNase I footprinting ARF1 - - StrukturderARF1Bindestelle ARF1 bindet scheinbar bevorzugt an den everted repeat Bereich der Palindromen AuxRE Sequenz Test mit mobility shift assay 37
38 StrukturderARF1Bindestelle(n) P3(1x) = 1 inverted repeat P3(2x) = 2 inverted repeats 1 everted repeat 1 x IRist nicht ausreichend für ARF1 Bindung 1 x ER kann ARF1binden 2 x ER = 2 ARF1Komplexe (P3(4x)) 38
39 StrukturderARF1Bindestelle ARF1bindet im evertedrepeatbereich der Palindromen AuxRE Sequenz bei GREsist der Abstand zwischen den Palindromen wichtig für die Bindungsaffinität Auch bei AuxREs? 39
40 quantitativergus assay Abstand 0 (ER0) 9 (ER9) Basen ER Konstrukte + GUS Protoplasten Auxin responseist am stärksten, wenn der Abstand der ERs7 bis 8 Basen beträgt 40
41 2.paper Science (1997) Fazit: COOH ARF1 NH 2 VP1/ ABI3homol. IV III ARF1 Bindingprotein AuxRE 41
42 Modelle(1997) ARF1 BP? BP? ARF1 BP? ARF1 BP? ARF1 42
43 nächstewoche: Alexandra und Ariane: 43
2. Seminar:
 2. Seminar: 29.04.2009 1. Ballaset al. (1993): Identification of the Auxin-responsive Element, AuxRE, in the Primary indoleacetic Acid-inducible Gene, PS- IAA4/5, of Pea (Pisumsativum). J Mol Biol 233:
2. Seminar: 29.04.2009 1. Ballaset al. (1993): Identification of the Auxin-responsive Element, AuxRE, in the Primary indoleacetic Acid-inducible Gene, PS- IAA4/5, of Pea (Pisumsativum). J Mol Biol 233:
2. Seminar:
 2. Seminar: 04.05.2010 1. Ballaset al. (1993): Identification of the Auxin-responsive Element, AuxRE, in the Primary indoleacetic Acid-inducible Gene, PS- IAA4/5, of Pea (Pisumsativum). J Mol Biol 233:
2. Seminar: 04.05.2010 1. Ballaset al. (1993): Identification of the Auxin-responsive Element, AuxRE, in the Primary indoleacetic Acid-inducible Gene, PS- IAA4/5, of Pea (Pisumsativum). J Mol Biol 233:
Hypothetisches Modell der letzten Papers
 Hypothetisches Modell der letzten Papers Bis dahin bekannt (1997) : - Induktion der Zellelongation durch Auxin -Auxin-responsiveGene untereinander hohe Homologie - Promotorsequenz für Auxin response in
Hypothetisches Modell der letzten Papers Bis dahin bekannt (1997) : - Induktion der Zellelongation durch Auxin -Auxin-responsiveGene untereinander hohe Homologie - Promotorsequenz für Auxin response in
General Concepts to Dissect Signaling Pathways
 General Concepts to Dissect Signaling Pathways Forward Genetics Molecular Biology Biochemistry Receptors Early Genes Growth & Development Gene Expression Binding Proteins ( Biochemistry) ( Reverse Genetics)
General Concepts to Dissect Signaling Pathways Forward Genetics Molecular Biology Biochemistry Receptors Early Genes Growth & Development Gene Expression Binding Proteins ( Biochemistry) ( Reverse Genetics)
VORANGEGANGENE MODELLE
 VORANGEGANGENE MODELLE UNSER THEMA HEUTE Ziel dieses Papers: - Nähere Charakterisierung der AuxREs - Analyse eines zu den AuxREs gehörenden Transkriptionsfaktors WAS BEREITS BEKANNT WAR: - Auxin moduliert
VORANGEGANGENE MODELLE UNSER THEMA HEUTE Ziel dieses Papers: - Nähere Charakterisierung der AuxREs - Analyse eines zu den AuxREs gehörenden Transkriptionsfaktors WAS BEREITS BEKANNT WAR: - Auxin moduliert
Molekulare Mechanismen der Signaltransduktion
 Molekulare Mechanismen der Signaltransduktion 07 - Identifizierung von ARF1 + Hinweise für Vorträge Folien: http://tinyurl.com/modul-mms http://www.pnas.org/content/111/14/5427/f1.large.jpg neues Modell
Molekulare Mechanismen der Signaltransduktion 07 - Identifizierung von ARF1 + Hinweise für Vorträge Folien: http://tinyurl.com/modul-mms http://www.pnas.org/content/111/14/5427/f1.large.jpg neues Modell
The auxin-insensitive bodenlos mutation affects primary root formation and apicalbasal patterning in the Arabidopsis embryo
 The auxin-insensitive bodenlos mutation affects primary root formation and apicalbasal patterning in the Arabidopsis embryo Thorsten Hamann, Ulrike Mayer and Gerd Jürgens The Arabidopsis BODENLOS gene
The auxin-insensitive bodenlos mutation affects primary root formation and apicalbasal patterning in the Arabidopsis embryo Thorsten Hamann, Ulrike Mayer and Gerd Jürgens The Arabidopsis BODENLOS gene
Molekulare Mechanismen der Signaltransduktion. 06 - Kartierung des AXR1 Gens + early auxin-induced genes Folien: http://tinyurl.
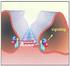 Molekulare Mechanismen der Signaltransduktion 06 - Kartierung des AXR1 Gens + early auxin-induced genes Folien: http://tinyurl.com/modul-mms bisheriges Modell auxin auxin AXR1 auxin response AXR1 potentieller
Molekulare Mechanismen der Signaltransduktion 06 - Kartierung des AXR1 Gens + early auxin-induced genes Folien: http://tinyurl.com/modul-mms bisheriges Modell auxin auxin AXR1 auxin response AXR1 potentieller
Hypothetische Modelle
 Hypothetische Modelle Heutiges Paper Vorgehensweise: Screening nach neuen Mutanten mit neuen Phänotyp Neuer Phänotyp: CPD, NPA- Resistenz (CPD, NPA: Wachstumshemmung durch Inhibierung des Auxin- Transport
Hypothetische Modelle Heutiges Paper Vorgehensweise: Screening nach neuen Mutanten mit neuen Phänotyp Neuer Phänotyp: CPD, NPA- Resistenz (CPD, NPA: Wachstumshemmung durch Inhibierung des Auxin- Transport
Abbildungs- und Tabellenverzeichnis Abkürzungsverzeichnis Genbezeichnung. 1. Einleitung 1
 Abbildungs- und Tabellenverzeichnis Abkürzungsverzeichnis Genbezeichnung VI VIII X 1. Einleitung 1 1.1 Das Plastom 1 1.2 Transkription in Chloroplasten 4 1.2.1 Die plastidäre Transkriptionsmaschinerie
Abbildungs- und Tabellenverzeichnis Abkürzungsverzeichnis Genbezeichnung VI VIII X 1. Einleitung 1 1.1 Das Plastom 1 1.2 Transkription in Chloroplasten 4 1.2.1 Die plastidäre Transkriptionsmaschinerie
Hypothetisches Modell
 Hypothetisches Modell Das Heutige Paper Inhalt: SCF bindet Auxin direkt TIR1 ist ein Auxin Rezeptor Auxin bindet direkt an TIR1, es sind keine zusätzlichen Komponenten nötig Methode Normales Pull down
Hypothetisches Modell Das Heutige Paper Inhalt: SCF bindet Auxin direkt TIR1 ist ein Auxin Rezeptor Auxin bindet direkt an TIR1, es sind keine zusätzlichen Komponenten nötig Methode Normales Pull down
The Arabidopsis F-box protein TIR1 is an auxin receptor. Von Stefan Kepinski & Ottoline Leyser
 The Arabidopsis F-box protein TIR1 is an auxin receptor Von Stefan Kepinski & Ottoline Leyser Bekanntes Modell Was war bekannt? In der Zwischenzeit gefunden: - ABP1 kann große Mengen Auxin binden und ist
The Arabidopsis F-box protein TIR1 is an auxin receptor Von Stefan Kepinski & Ottoline Leyser Bekanntes Modell Was war bekannt? In der Zwischenzeit gefunden: - ABP1 kann große Mengen Auxin binden und ist
Identifikation einer neuen WRKY-Transkriptionsfaktorbindungsstelle. in bioinformatisch identifizierten,
 Identifikation einer neuen WRKY-Transkriptionsfaktorbindungsstelle in bioinformatisch identifizierten, Pathogen-responsiven c/s-elementen aus Arabidopsis thaliana Von der Fakultät für Lebenswissenschaften
Identifikation einer neuen WRKY-Transkriptionsfaktorbindungsstelle in bioinformatisch identifizierten, Pathogen-responsiven c/s-elementen aus Arabidopsis thaliana Von der Fakultät für Lebenswissenschaften
Hypothetische Modelle
 Hypothetische Modelle Hypothetische Modelle Das Paper Identification of an SCF ubiquitin ligase complex required for auxin response in Arabidopsis thaliana William M. Gray,1,4 J. Carlos del Pozo,1,4 Loni
Hypothetische Modelle Hypothetische Modelle Das Paper Identification of an SCF ubiquitin ligase complex required for auxin response in Arabidopsis thaliana William M. Gray,1,4 J. Carlos del Pozo,1,4 Loni
Stand von letzter Woche
 RUB ECR1 AXR1 Stand von letzter Woche E2 U? E1-like AXR1 Repressor ARF1 Proteasom AuxRE Repressor wird sehr schnell abgebaut notwendig für Auxinantwort evtl. Substrat für SCF Identifikation des SCF-Ubiquitin
RUB ECR1 AXR1 Stand von letzter Woche E2 U? E1-like AXR1 Repressor ARF1 Proteasom AuxRE Repressor wird sehr schnell abgebaut notwendig für Auxinantwort evtl. Substrat für SCF Identifikation des SCF-Ubiquitin
Präsentiert von Christina Staudigl
 Präsentiert von Christina Staudigl Was bisher geschah 2 Was bisher geschah Neues aus der Signaltransduktion? - nichts wirklich grundlegendes Aber: mehr ARFs gefunden (10x) mit leichten Unterschieden in
Präsentiert von Christina Staudigl Was bisher geschah 2 Was bisher geschah Neues aus der Signaltransduktion? - nichts wirklich grundlegendes Aber: mehr ARFs gefunden (10x) mit leichten Unterschieden in
Entwicklungs /gewebespezifische Genexpression
 Übung 11 Genregulation bei Prokaryoten Konzepte: Entwicklungs /gewebespezifische Genexpression Positive Genregulation Negative Genregulation cis /trans Regulation 1. Auf welchen Ebenen kann Genregulation
Übung 11 Genregulation bei Prokaryoten Konzepte: Entwicklungs /gewebespezifische Genexpression Positive Genregulation Negative Genregulation cis /trans Regulation 1. Auf welchen Ebenen kann Genregulation
Seminar. Leibniz Institut für Pflanzenbiochemie
 Seminar Molekulare l Mechanismen der Signaltransduktion Marcel lquint Leibniz Institut für Pflanzenbiochemie Abiotic stimuli Light Temperature Wind Drought Rain etc., rapid response essential Biotic stimuli
Seminar Molekulare l Mechanismen der Signaltransduktion Marcel lquint Leibniz Institut für Pflanzenbiochemie Abiotic stimuli Light Temperature Wind Drought Rain etc., rapid response essential Biotic stimuli
Entwicklungs /gewebespezifische Genexpression. Coexpression funktional überlappender Gene
 Übung 11 Genregulation bei Prokaryoten Konzepte: Entwicklungs /gewebespezifische Genexpression Coexpression funktional überlappender Gene Positive Genregulation Negative Genregulation cis /trans Regulation
Übung 11 Genregulation bei Prokaryoten Konzepte: Entwicklungs /gewebespezifische Genexpression Coexpression funktional überlappender Gene Positive Genregulation Negative Genregulation cis /trans Regulation
Transkription Teil 2. - Transkription bei Eukaryoten -
 Transkription Teil 2 - Transkription bei Eukaryoten - Inhalte: Unterschiede in der Transkription von Pro- und Eukaryoten Die RNA-Polymerasen der Eukaryoten Cis- und trans-aktive Elemente Promotoren Transkriptionsfaktoren
Transkription Teil 2 - Transkription bei Eukaryoten - Inhalte: Unterschiede in der Transkription von Pro- und Eukaryoten Die RNA-Polymerasen der Eukaryoten Cis- und trans-aktive Elemente Promotoren Transkriptionsfaktoren
Übung 11 Genregulation bei Prokaryoten
 Übung 11 Genregulation bei Prokaryoten Konzepte: Differentielle Genexpression Positive Genregulation Negative Genregulation cis-/trans-regulation 1. Auf welchen Ebenen kann Genregulation stattfinden? Definition
Übung 11 Genregulation bei Prokaryoten Konzepte: Differentielle Genexpression Positive Genregulation Negative Genregulation cis-/trans-regulation 1. Auf welchen Ebenen kann Genregulation stattfinden? Definition
Übung 11 Genregulation bei Prokaryoten
 Übung 11 Genregulation bei Prokaryoten Konzepte: Differentielle Genexpression Positive Genregulation Negative Genregulation cis-/trans-regulation 1. Auf welchen Ebenen kann Genregulation stattfinden? Definition
Übung 11 Genregulation bei Prokaryoten Konzepte: Differentielle Genexpression Positive Genregulation Negative Genregulation cis-/trans-regulation 1. Auf welchen Ebenen kann Genregulation stattfinden? Definition
AlgoBio WS 16/17 Protein-DNA Interaktionen ChiP-Seq Datenanalyse. Annalisa Marsico
 AlgoBio WS 16/17 Protein-DNA Interaktionen ChiP-Seq Datenanalyse Annalisa Marsico 6.02.2017 Protein-DNA Interaktionen Häufig binden sich Proteine an DNA, um ihre biologische Funktion zu regulieren. Transkriptionsfaktoren
AlgoBio WS 16/17 Protein-DNA Interaktionen ChiP-Seq Datenanalyse Annalisa Marsico 6.02.2017 Protein-DNA Interaktionen Häufig binden sich Proteine an DNA, um ihre biologische Funktion zu regulieren. Transkriptionsfaktoren
KV: Genexpression und Transkription Michael Altmann
 Institut für Biochemie und Molekulare Medizin KV: Genexpression und Transkription Michael Altmann Herbstsemester 2008/2009 Übersicht VL Genexpression / Transkription 1.) Was ist ein Gen? 2.) Welche Arten
Institut für Biochemie und Molekulare Medizin KV: Genexpression und Transkription Michael Altmann Herbstsemester 2008/2009 Übersicht VL Genexpression / Transkription 1.) Was ist ein Gen? 2.) Welche Arten
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
Regulation der Genexpression: regulierbare Promotoren, Proteine und sirna
 Regulation der Genexpression: regulierbare Promotoren, Proteine und sirna Biochemie Praktikum Christian Brendel, AG Grez Ebenen der Genregulation in Eukaryoten Cytoplasma DNA Zellkern Introns Exons Chromatin
Regulation der Genexpression: regulierbare Promotoren, Proteine und sirna Biochemie Praktikum Christian Brendel, AG Grez Ebenen der Genregulation in Eukaryoten Cytoplasma DNA Zellkern Introns Exons Chromatin
Multifunktionale DNA Kassetten zur konditionalen Mutagenese in der Maus
 Multifunktionale DNA Kassetten zur konditionalen Mutagenese in der Maus Von der Fakultat fur Lebenswissenschaften der Technischen Universitat Carolo-Wilhelmina zu Braunschweig zur Erlangung des Grades
Multifunktionale DNA Kassetten zur konditionalen Mutagenese in der Maus Von der Fakultat fur Lebenswissenschaften der Technischen Universitat Carolo-Wilhelmina zu Braunschweig zur Erlangung des Grades
Vortrag von Philipp Nerke und Bruno Voigt
 Vortrag von Philipp Nerke und Bruno Voigt Was war bekannt? Wirkung von Auxin Streckungswachstum Apicaldominanz Gravitropismus Laterales Wurzelwachstum Bekannte Gene der Auxin-Regulation AXR1 AXR4 AUX1
Vortrag von Philipp Nerke und Bruno Voigt Was war bekannt? Wirkung von Auxin Streckungswachstum Apicaldominanz Gravitropismus Laterales Wurzelwachstum Bekannte Gene der Auxin-Regulation AXR1 AXR4 AUX1
Grundlegende Experimente der Molekulargenetik
 Übung 12 Wiederholung/Zusatzübung Inhalte: Mendelscher Erbgang Grundlegende Experimente der Molekulargenetik Transposons Methoden 1. Sie haben drei runde, gelbe Erbsen (A, B und C). Aus jeder der drei
Übung 12 Wiederholung/Zusatzübung Inhalte: Mendelscher Erbgang Grundlegende Experimente der Molekulargenetik Transposons Methoden 1. Sie haben drei runde, gelbe Erbsen (A, B und C). Aus jeder der drei
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 3. Aus welchen vier Nukleotiden ist RNA aufgebaut? 4. DNA RNA 5. Ein Wissenschaftler
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 3. Aus welchen vier Nukleotiden ist RNA aufgebaut? 4. DNA RNA 5. Ein Wissenschaftler
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
Eukaryontische DNA-Bindedomänen
 1. Viele eukaryotische (und auch prokaryotische) Transkriptionsfaktoren besitzen eine DNA-bindende Domäne, die an eine ganz bestimmte DNA- Sequenz binden kann. Aufgrund von Ähnlichkeiten in der Struktur
1. Viele eukaryotische (und auch prokaryotische) Transkriptionsfaktoren besitzen eine DNA-bindende Domäne, die an eine ganz bestimmte DNA- Sequenz binden kann. Aufgrund von Ähnlichkeiten in der Struktur
genehmigte Di s sert ation von Klaus Schmidt aus Groß Lafferde
 Identifizierung eines Cercospora beticola responsiven Bereichs innerhalb des Kernpromotors despa/-gens der Zuckerrübe sowie eines daran bindenden, neuen Transkriptionsfaktors Von der Gemeinsamen Naturwissenschaftlichen
Identifizierung eines Cercospora beticola responsiven Bereichs innerhalb des Kernpromotors despa/-gens der Zuckerrübe sowie eines daran bindenden, neuen Transkriptionsfaktors Von der Gemeinsamen Naturwissenschaftlichen
Seminar Molekulare Mechanismen der Signaltransduktion
 Seminar Molekulare Mechanismen der Signaltransduktion Gliederung (22.04.2009): Allgemeine Einleitung (Auxin, Nomenklatur...) Vorstellung der ersten paper Termine verteilen 1. Estelle and Somerville, (1987)
Seminar Molekulare Mechanismen der Signaltransduktion Gliederung (22.04.2009): Allgemeine Einleitung (Auxin, Nomenklatur...) Vorstellung der ersten paper Termine verteilen 1. Estelle and Somerville, (1987)
Kulturen von humanen Nabelschnur-Endothelzellen (HUVEC) produzieren konstant Endothelin-1 (ET-1) und geben dieses in das Kulturmedium ab.
 4 ERGEBNISSE 4.1 Endothelin Kulturen von humanen Nabelschnur-Endothelzellen (HUVEC) produzieren konstant Endothelin-1 (ET-1) und geben dieses in das Kulturmedium ab. 4.1.1 Dosisabhängige Herabregulation
4 ERGEBNISSE 4.1 Endothelin Kulturen von humanen Nabelschnur-Endothelzellen (HUVEC) produzieren konstant Endothelin-1 (ET-1) und geben dieses in das Kulturmedium ab. 4.1.1 Dosisabhängige Herabregulation
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 4 (20.06. 24.06.) Regulation der Transkription II, Translation
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 4 (20.06. 24.06.) Regulation der Transkription II, Translation
Genexpressionsregulation
 Genexpressionsregulation Genexpressionsregulation Different tissue types 1 2 3 4 5 6 7 8 Taken from Caron et al., 2001 Verschiedene Ebenen der Genexpressionsregulation Epigenetic mechanisms Transkriptionskontrolle
Genexpressionsregulation Genexpressionsregulation Different tissue types 1 2 3 4 5 6 7 8 Taken from Caron et al., 2001 Verschiedene Ebenen der Genexpressionsregulation Epigenetic mechanisms Transkriptionskontrolle
Das Paper von heute. Samuel Grimm & Jan Kemna
 Das Paper von heute Samuel Grimm & Jan Kemna Bisheriges Modell Was bereits bekannt war - TIR1 ist an Auxinantwort (Zellteilung, Elongation, Differenzierung) beteiligt, im selben Signalweg wie AXR1 - TIR1
Das Paper von heute Samuel Grimm & Jan Kemna Bisheriges Modell Was bereits bekannt war - TIR1 ist an Auxinantwort (Zellteilung, Elongation, Differenzierung) beteiligt, im selben Signalweg wie AXR1 - TIR1
3 Ergebnisse. 3.1 Die Speckling-Domäne von Wt1 umfaßt die Aminosäuren
 3 Ergebnisse 3.1 Die Speckling-Domäne von Wt1 umfaßt die Aminosäuren 76-120 Die Existenz verschiedener Isoformen von WT1 ist unter anderem auf die Verwendung einer für die Aminosäuren KTS kodierenden alternativen
3 Ergebnisse 3.1 Die Speckling-Domäne von Wt1 umfaßt die Aminosäuren 76-120 Die Existenz verschiedener Isoformen von WT1 ist unter anderem auf die Verwendung einer für die Aminosäuren KTS kodierenden alternativen
Die Initiation der Transkription in den Mitochondrien höherer Pflanzen
 Die Initiation der Transkription in den Mitochondrien höherer Pflanzen DISSERTATION zur Erlangung des Grades eines Doktors der Naturwissenschaften am Fachbereich Chemie der Freien Universität Berlin vorgelegt
Die Initiation der Transkription in den Mitochondrien höherer Pflanzen DISSERTATION zur Erlangung des Grades eines Doktors der Naturwissenschaften am Fachbereich Chemie der Freien Universität Berlin vorgelegt
2.1 Das prä-mrna Spleißen 3
 I 1. Zusammenfassung 1 2. Einleitung 3 2.1 Das prä-mrna Spleißen 3 2.1.1 Die Konsensussequenzen zweier Klassen von prä-mrna Introns 3 2.1.2 Die katalytischen Transesterifizierungsreaktionen 5 2.2 Das U2-abhängige
I 1. Zusammenfassung 1 2. Einleitung 3 2.1 Das prä-mrna Spleißen 3 2.1.1 Die Konsensussequenzen zweier Klassen von prä-mrna Introns 3 2.1.2 Die katalytischen Transesterifizierungsreaktionen 5 2.2 Das U2-abhängige
Elektronenmikroskopie zeigte die Existenz der A-, P- und E- trna-bindungsstellen. Abb. aus Stryer (5th Ed.)
 Elektronenmikroskopie zeigte die Existenz der A-, P- und E- trna-bindungsstellen Die verschiedenen Ribosomen-Komplexe können im Elektronenmikroskop beobachtet werden Durch Röntgenkristallographie wurden
Elektronenmikroskopie zeigte die Existenz der A-, P- und E- trna-bindungsstellen Die verschiedenen Ribosomen-Komplexe können im Elektronenmikroskop beobachtet werden Durch Röntgenkristallographie wurden
Promotor kodierende Sequenz Terminator
 5.2 Genexpression Sequenz in eine RNA-Sequenz. Die Enzyme, die diese Reaktion katalysieren, sind die DNA-abhängigen RNA-Polymerasen. Sie bestehen aus mehreren Untereinheiten, die von den Pro- bis zu den
5.2 Genexpression Sequenz in eine RNA-Sequenz. Die Enzyme, die diese Reaktion katalysieren, sind die DNA-abhängigen RNA-Polymerasen. Sie bestehen aus mehreren Untereinheiten, die von den Pro- bis zu den
Molekulargenetik der Eukaryoten WS 2014/15, VL 11. Erwin R. Schmidt Institut für Molekulargenetik
 Molekulargenetik der Eukaryoten WS 2014/15, VL 11 Erwin R. Schmidt Institut für Molekulargenetik Abhängig von der Genklasse: Genstruktur der Eukaryoten 1. RNA Pol I Gene: 18S, 5,8S, 28S rrna 2. RNA Pol
Molekulargenetik der Eukaryoten WS 2014/15, VL 11 Erwin R. Schmidt Institut für Molekulargenetik Abhängig von der Genklasse: Genstruktur der Eukaryoten 1. RNA Pol I Gene: 18S, 5,8S, 28S rrna 2. RNA Pol
Gibt es zwei Klassen von Promotoren? Are there two classes of promoters?
 Gibt es zwei Klassen von Promotoren? Are there two classes of promoters? Vingron, Martin Max-Planck-Institut für molekulare Genetik, Berlin Korrespondierender Autor E-Mail: vingron@molgen.mpg.de Zusammenfassung
Gibt es zwei Klassen von Promotoren? Are there two classes of promoters? Vingron, Martin Max-Planck-Institut für molekulare Genetik, Berlin Korrespondierender Autor E-Mail: vingron@molgen.mpg.de Zusammenfassung
TRANSKRIPTION I. Die Herstellung von RNA bei E-Coli
 TRANSKRIPTION I Die Herstellung von RNA bei E-Coli Inhalt Aufbau der RNA-Polymerase Promotoren Sigma-Untereinheit Entwindung der DNA Elongation Termination der Transkription Modifizierung der RNA Antibiotika
TRANSKRIPTION I Die Herstellung von RNA bei E-Coli Inhalt Aufbau der RNA-Polymerase Promotoren Sigma-Untereinheit Entwindung der DNA Elongation Termination der Transkription Modifizierung der RNA Antibiotika
Seminar Molekulare Mechanismen der Signaltransduktion
 Seminar Molekulare Mechanismen der Signaltransduktion Gliederung (27.04.2010): Allgemeine Einleitung (Auxin, Nomenklatur...) Vorstellung der ersten paper Termine verteilen 1. Estelle and Somerville, (1987)
Seminar Molekulare Mechanismen der Signaltransduktion Gliederung (27.04.2010): Allgemeine Einleitung (Auxin, Nomenklatur...) Vorstellung der ersten paper Termine verteilen 1. Estelle and Somerville, (1987)
Transkription und Translation sind in Eukaryoten räumlich und zeitlich getrennt. Abb. aus Stryer (5th Ed.)
 Transkription und Translation sind in Eukaryoten räumlich und zeitlich getrennt Die Initiation der Translation bei Eukaryoten Der eukaryotische Initiationskomplex erkennt zuerst das 5 -cap der mrna und
Transkription und Translation sind in Eukaryoten räumlich und zeitlich getrennt Die Initiation der Translation bei Eukaryoten Der eukaryotische Initiationskomplex erkennt zuerst das 5 -cap der mrna und
Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR)
 PCR Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR) von Kary B. Mullis entwickelt (1985) eigentlich im Mai 1983 bei einer nächtlichen Autofahrt erstes erfolgreiches Experiment am 16.12.1983
PCR Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR) von Kary B. Mullis entwickelt (1985) eigentlich im Mai 1983 bei einer nächtlichen Autofahrt erstes erfolgreiches Experiment am 16.12.1983
Drosophila melanogaster
 Modul biol113 Zellbiologie Drosophila melanogaster Komponenten der angeborenen Immunabwehr Experimente 1) RT (Reverse Transkriptase)-PCR zum Nachweis einer AMP- Expression nach Infektion 1.1 PCR-Reaktion
Modul biol113 Zellbiologie Drosophila melanogaster Komponenten der angeborenen Immunabwehr Experimente 1) RT (Reverse Transkriptase)-PCR zum Nachweis einer AMP- Expression nach Infektion 1.1 PCR-Reaktion
Praktikum der Molekulargenetik
 Ulrich Kück (Hrsg.) Praktikum der Molekulargenetik unter der Mitarbeit von A. Bunse, H. Holländer-Czytko, S. Jeske, C. Klämbt, R. Klapper, I. Kubigsteltig, F. Meinhardt, J. Nickelsen, M. Nowrousian, S.
Ulrich Kück (Hrsg.) Praktikum der Molekulargenetik unter der Mitarbeit von A. Bunse, H. Holländer-Czytko, S. Jeske, C. Klämbt, R. Klapper, I. Kubigsteltig, F. Meinhardt, J. Nickelsen, M. Nowrousian, S.
Genregulation in Bakterien. Das LAC Operon
 Genregulation in Bakterien Das LAC Operon Der Fluss der genetischen Information Transkription Translation DNA mrna Protein Replikation (Reverse Transkription) Modifikation DNA Funktionelles Protein Horizontaler
Genregulation in Bakterien Das LAC Operon Der Fluss der genetischen Information Transkription Translation DNA mrna Protein Replikation (Reverse Transkription) Modifikation DNA Funktionelles Protein Horizontaler
Promotoren und Transkriptionsfaktoren (TF)
 Promotoren und Transkriptionsfaktoren (TF) Übersicht Promoteranalyse Transiente Genexpression DNA/TF Bindung TFs in Eukaryoten Anzahl Klassen Domain shuffling Kombinatorische Kontrolle Methoden zur Isolation
Promotoren und Transkriptionsfaktoren (TF) Übersicht Promoteranalyse Transiente Genexpression DNA/TF Bindung TFs in Eukaryoten Anzahl Klassen Domain shuffling Kombinatorische Kontrolle Methoden zur Isolation
Wiebke Häger Molekulare Zellbiologie und Biomedizin (Seminar: Zelluläre Plastizität) WS 2012/2013
 Wiebke Häger Molekulare Zellbiologie und Biomedizin (Seminar: Zelluläre Plastizität) WS 2012/2013 Embryonale Stammzellen (ESC) Befruchtung, 2-, 4-, 8-Zellstadium, Morula, Blastula Embryoblast = innere
Wiebke Häger Molekulare Zellbiologie und Biomedizin (Seminar: Zelluläre Plastizität) WS 2012/2013 Embryonale Stammzellen (ESC) Befruchtung, 2-, 4-, 8-Zellstadium, Morula, Blastula Embryoblast = innere
Praktikum Biochemie B.Sc. Water Science WS Enzymregulation. Marinja Niggemann, Denise Schäfer
 Praktikum Biochemie B.Sc. Water Science WS 2011 Enzymregulation Marinja Niggemann, Denise Schäfer Regulatorische Strategien 1. Allosterische Wechselwirkung 2. Proteolytische Aktivierung 3. Kovalente Modifikation
Praktikum Biochemie B.Sc. Water Science WS 2011 Enzymregulation Marinja Niggemann, Denise Schäfer Regulatorische Strategien 1. Allosterische Wechselwirkung 2. Proteolytische Aktivierung 3. Kovalente Modifikation
Kaninchen: 1 cagattgaggagagcaccaccatcgtcacctcgcagttggcggaggtcagcgcagccgag 60
 Ergebnisse 6 3. Ergebnisse 3. Charakterisierung der zelllinienspezifischen cdn Die Entwicklung zweier Zelllinien, des epithelialen Trophoblasten und des pluripotenten Embryoblasten, ist der erste Differenzierungsschritt
Ergebnisse 6 3. Ergebnisse 3. Charakterisierung der zelllinienspezifischen cdn Die Entwicklung zweier Zelllinien, des epithelialen Trophoblasten und des pluripotenten Embryoblasten, ist der erste Differenzierungsschritt
Inhalt 1 Modellorganismen
 Inhalt 1 Modellorganismen....................................... 1 1.1 Escherichia coli....................................... 1 1.1.1 Historisches...................................... 3 1.1.2 Lebenszyklus.....................................
Inhalt 1 Modellorganismen....................................... 1 1.1 Escherichia coli....................................... 1 1.1.1 Historisches...................................... 3 1.1.2 Lebenszyklus.....................................
Institut für Biochemie und Molekulare Medizin. Lecture 1 Translational components. Michael Altmann FS 2011
 Institut für Biochemie und Molekulare Medizin Lecture 1 Translational components Michael Altmann FS 2011 Gene Expression Fliessdiagramm der eukaryotischen Genexpression Die Expression eines Gens kann auf
Institut für Biochemie und Molekulare Medizin Lecture 1 Translational components Michael Altmann FS 2011 Gene Expression Fliessdiagramm der eukaryotischen Genexpression Die Expression eines Gens kann auf
The TIR1 protein of Arabidopsis functions in auxin response and is related to human SKP2 and
 The TIR1 protein of Arabidopsis functions in auxin response and is related to human SKP2 and yeast Grr1p Publikation von Max Ruegger, Elizabeth Dewey, William M. Gray, Lawrence Hobbie, Jocelyn Turner und
The TIR1 protein of Arabidopsis functions in auxin response and is related to human SKP2 and yeast Grr1p Publikation von Max Ruegger, Elizabeth Dewey, William M. Gray, Lawrence Hobbie, Jocelyn Turner und
Genaktivierung und Genexpression
 Genaktivierung und Genexpression Unter Genexpression versteht man ganz allgemein die Ausprägung des Genotyps zum Phänotyp einer Zelle oder eines ganzen Organismus. Genotyp: Gesamtheit der Informationen
Genaktivierung und Genexpression Unter Genexpression versteht man ganz allgemein die Ausprägung des Genotyps zum Phänotyp einer Zelle oder eines ganzen Organismus. Genotyp: Gesamtheit der Informationen
Proteasom* Funktion und Kennedy Syndrom (SBMA)
 Proteasom* Funktion und Kennedy Syndrom (SBMA) Vorgetragen durch: Lenore K. Beitel, Ph.D. Forschungswissenschaftlerin Lady Davis Institute for Medical Research Montreal, Canada * Begriffsbedeutung siehe
Proteasom* Funktion und Kennedy Syndrom (SBMA) Vorgetragen durch: Lenore K. Beitel, Ph.D. Forschungswissenschaftlerin Lady Davis Institute for Medical Research Montreal, Canada * Begriffsbedeutung siehe
Master-Modul Molekulare Pflanzenphysiologie
 Master-Modul Molekulare Pflanzenphysiologie Was macht BES1? Die Lokalisation zeigte bereits an, dass BES1 das BL- Signal in den Kern überträgt. Microarray-Experimente hatten gezeigt, dass BES1 BLresponsive
Master-Modul Molekulare Pflanzenphysiologie Was macht BES1? Die Lokalisation zeigte bereits an, dass BES1 das BL- Signal in den Kern überträgt. Microarray-Experimente hatten gezeigt, dass BES1 BLresponsive
Posttranskriptionale Veränderungen der Genexpression bei hereditären Erkrankungen
 Posttranskriptionale Veränderungen der Genexpression bei hereditären Erkrankungen Dissertation zur Erlangung des Doktorgrades Dr. rer. nat. des Fachbereichs Biologie, Chemie, Pharmazie der Freien Universität
Posttranskriptionale Veränderungen der Genexpression bei hereditären Erkrankungen Dissertation zur Erlangung des Doktorgrades Dr. rer. nat. des Fachbereichs Biologie, Chemie, Pharmazie der Freien Universität
Evolutionäre Verfahren 3 : Yeast Two Hybrid System. Biochemiepraktikum II WS 2007/ Januar Februar 2008
 Evolutionäre Verfahren 3 : Yeast Two Hybrid System Biochemiepraktikum II WS 2007/2008 15. Januar 2008 5. Februar 2008 AG Bernd Groner Corina Heinz Astrid Weiß Protein-Protein Interaktionen Protein-Protein
Evolutionäre Verfahren 3 : Yeast Two Hybrid System Biochemiepraktikum II WS 2007/2008 15. Januar 2008 5. Februar 2008 AG Bernd Groner Corina Heinz Astrid Weiß Protein-Protein Interaktionen Protein-Protein
Funktion. Transkriptionsfaktor in der Ethylen-Signaltransduktion
 Modifiziertes Funktion Funktionen Protein des Target Ubiquitinierung Phytochrom Polyubi.: (Ubiquitylierung) AUX/IAA EIN2 Auxin-Signaltransduktion Transkriptionsfaktor in der Ethylen-Signaltransduktion
Modifiziertes Funktion Funktionen Protein des Target Ubiquitinierung Phytochrom Polyubi.: (Ubiquitylierung) AUX/IAA EIN2 Auxin-Signaltransduktion Transkriptionsfaktor in der Ethylen-Signaltransduktion
3.2 Posttranslationelle Modifikation von Wt1 durch Phosphorylierung
 3.2 Posttranslationelle Modifikation von Wt1 durch Phosphorylierung Transkriptionsfaktoren erfahren oft eine posttranslationelle Modifikation in Form von Phosphorylierung und werden dadurch in ihrer Aktivität
3.2 Posttranslationelle Modifikation von Wt1 durch Phosphorylierung Transkriptionsfaktoren erfahren oft eine posttranslationelle Modifikation in Form von Phosphorylierung und werden dadurch in ihrer Aktivität
6. Induktion der Galactosidase von Escherichia coli
 Johannes Gutenberg-Universität Mainz Institut für Mikrobiologie und Weinforschung FI-Übung: Identifizierung, Wachstum und Regulation (WS 2004/05) Sebastian Lux Datum: 19.1.2005 6. Induktion der Galactosidase
Johannes Gutenberg-Universität Mainz Institut für Mikrobiologie und Weinforschung FI-Übung: Identifizierung, Wachstum und Regulation (WS 2004/05) Sebastian Lux Datum: 19.1.2005 6. Induktion der Galactosidase
3.2.1 Methodischer Ablauf zur Herstellung der Konstrukte für das mating based Split-Ubiquitin-System
 3.2.1 Methodischer Ablauf zur Herstellung der Konstrukte für das mating based plit-ubiquitin-ystem Durch die Expressionsanalysen mittels Promotor:GU-Fusion der einzelnen Mitglieder der 2-Genfamilie und
3.2.1 Methodischer Ablauf zur Herstellung der Konstrukte für das mating based plit-ubiquitin-ystem Durch die Expressionsanalysen mittels Promotor:GU-Fusion der einzelnen Mitglieder der 2-Genfamilie und
Zentrales Dogma der Biologie
 Zentrales Dogma der Biologie Transkription: von der DNA zur RNA Biochemie 01/1 Transkription Biochemie 01/2 Transkription DNA: RNA: Biochemie 01/3 Transkription DNA: RNA: Biochemie 01/4 Transkription RNA:
Zentrales Dogma der Biologie Transkription: von der DNA zur RNA Biochemie 01/1 Transkription Biochemie 01/2 Transkription DNA: RNA: Biochemie 01/3 Transkription DNA: RNA: Biochemie 01/4 Transkription RNA:
Georg-August-Universität Göttingen
 Georg-August-Universität Göttingen Abteilung für Allgemeine Mikrobiologie Institut für Mikrobiologie und Genetik Prof. Dr. Jörg Stülke Email:jstuelk@gwdg.de http://wwwuser.gwdg.de/~genmibio/stuelke.html
Georg-August-Universität Göttingen Abteilung für Allgemeine Mikrobiologie Institut für Mikrobiologie und Genetik Prof. Dr. Jörg Stülke Email:jstuelk@gwdg.de http://wwwuser.gwdg.de/~genmibio/stuelke.html
Untersuchungen zur Funktion von Stärke-Synthasen in der Kartoffel (Solanum tuberosum L.)
 Untersuchungen zur Funktion von Stärke-Synthasen in der Kartoffel (Solanum tuberosum L.) Inaugural-Dissertation Erlangung der Doktorwürde im Fachbereich Biologie der Freien Univeisität Berlin vorgelegt
Untersuchungen zur Funktion von Stärke-Synthasen in der Kartoffel (Solanum tuberosum L.) Inaugural-Dissertation Erlangung der Doktorwürde im Fachbereich Biologie der Freien Univeisität Berlin vorgelegt
AUFGABENSAMMLUNG. Restriktionsenzyme. Füllen Sie den Lückentext aus. Gentechnik Schroedel, Braunschweig
 Restriktionsenzyme Füllen Sie den Lückentext aus. PCR 1a Mit dem folgenden Quiz können Sie Ihr Wissen zum Thema PCR überprüfen. Klicken Sie jeweils die richtige Antwort an. PCR 1b Mit dem folgenden Quiz
Restriktionsenzyme Füllen Sie den Lückentext aus. PCR 1a Mit dem folgenden Quiz können Sie Ihr Wissen zum Thema PCR überprüfen. Klicken Sie jeweils die richtige Antwort an. PCR 1b Mit dem folgenden Quiz
Molekulargenetik der Eukaryoten WS 2014/15, VL 12. Erwin R. Schmidt Institut für Molekulargenetik
 Molekulargenetik der Eukaryoten WS 2014/15, V 12 Erwin R. Schmidt Institut für Molekulargenetik Der basale Transkriptionskomplex plus genspezifische TFs Zusammenfassung: Präinitiationskomplexe der verschiedenen
Molekulargenetik der Eukaryoten WS 2014/15, V 12 Erwin R. Schmidt Institut für Molekulargenetik Der basale Transkriptionskomplex plus genspezifische TFs Zusammenfassung: Präinitiationskomplexe der verschiedenen
Beitrag und Regulation der Tight Junctions zur Schutzfunktion der epidermalen Hautbarriere
 Beitrag und Regulation der Tight Junctions zur Schutzfunktion der epidermalen Hautbarriere Inaugural-Dissertation zur Erlangung des naturwissenschaftlichen Doktorgrades im Fachbereich Chemie der Universität
Beitrag und Regulation der Tight Junctions zur Schutzfunktion der epidermalen Hautbarriere Inaugural-Dissertation zur Erlangung des naturwissenschaftlichen Doktorgrades im Fachbereich Chemie der Universität
Musterlösung - Übung 5 Vorlesung Bio-Engineering Sommersemester 2008
 Aufgabe 1: Prinzipieller Ablauf der Proteinbiosynthese a) Erklären Sie folgende Begriffe möglichst in Ihren eigenen Worten (1 kurzer Satz): Gen Nukleotid RNA-Polymerase Promotor Codon Anti-Codon Stop-Codon
Aufgabe 1: Prinzipieller Ablauf der Proteinbiosynthese a) Erklären Sie folgende Begriffe möglichst in Ihren eigenen Worten (1 kurzer Satz): Gen Nukleotid RNA-Polymerase Promotor Codon Anti-Codon Stop-Codon
2.1 Die Entstehung des Gehirns aus neuralen Stammzellen Transkriptionsfaktoren in der Gehirnentwicklung...16
 Inhaltsverzeichnis Danksagung...3 Inhaltsverzeichnis...5 Abkürzungverzeichnis...1 1 Zielsetzung...4 2 Einleitung...6 2.1 Die Entstehung des Gehirns aus neuralen Stammzellen...6 2.2 Radiale Gliazellen...9
Inhaltsverzeichnis Danksagung...3 Inhaltsverzeichnis...5 Abkürzungverzeichnis...1 1 Zielsetzung...4 2 Einleitung...6 2.1 Die Entstehung des Gehirns aus neuralen Stammzellen...6 2.2 Radiale Gliazellen...9
Pharmazeutische Biologie WS2011/2012. Das neue Paradigma: Personalisierte Medizin
 3. Vorlesung Pharmazeutische Biologie WS2011/2012 Das neue Paradigma: Personalisierte Medizin Prof. Theo Dingermann Institut für Pharmazeutische Biologie Biozentrum Max-von Laue-Str. 9 60438 Frankfurt
3. Vorlesung Pharmazeutische Biologie WS2011/2012 Das neue Paradigma: Personalisierte Medizin Prof. Theo Dingermann Institut für Pharmazeutische Biologie Biozentrum Max-von Laue-Str. 9 60438 Frankfurt
Biochemisches Grundpraktikum
 Biochemisches Grundpraktikum Dr. Ellen Hornung; Email: ehornun@gwdg.de; Tel: 39-5748 Einteilung der Praktikumsplätze: Eintragen in Listen am - Dienstag, 10.11.2009, von 12:00 13:00 - Freitag, 13.11.2009,
Biochemisches Grundpraktikum Dr. Ellen Hornung; Email: ehornun@gwdg.de; Tel: 39-5748 Einteilung der Praktikumsplätze: Eintragen in Listen am - Dienstag, 10.11.2009, von 12:00 13:00 - Freitag, 13.11.2009,
Die doppelsträngige Helix wird zunächst aufgetrennt. Enzym: Helicase (ATP-abhängig)
 Die doppelsträngige Helix wird zunächst aufgetrennt. Enzym: Helicase (ATP-abhängig) Die doppelsträngige Helix wird zunächst aufgetrennt. Enzym: Helicase (ATP-abhängig) Jetzt liegen diese Stränge einzeln
Die doppelsträngige Helix wird zunächst aufgetrennt. Enzym: Helicase (ATP-abhängig) Die doppelsträngige Helix wird zunächst aufgetrennt. Enzym: Helicase (ATP-abhängig) Jetzt liegen diese Stränge einzeln
Musterstudent, Fredy
 Musterstudent, Fredy Zellwandassoziiertes Protein Teichonsäure Lipoteichonsäure Murein (Peptidoglycan) Cytoplasmamembran Membranprotein O- Polysaccharid Core- Polysaccharid Lipid A repeating unit Membranproteinkomplex
Musterstudent, Fredy Zellwandassoziiertes Protein Teichonsäure Lipoteichonsäure Murein (Peptidoglycan) Cytoplasmamembran Membranprotein O- Polysaccharid Core- Polysaccharid Lipid A repeating unit Membranproteinkomplex
Zellstreckung/Phototropismus
 Zellstreckung/Phototropismus Phototropismus Zeitrafferaufnahmen von Haferkoleoptilen, die von links mit Blaulicht bestrahlt wurden. Effektiv: Blaulicht Krümmung erfolgt durch Zellstreckung auf der dem
Zellstreckung/Phototropismus Phototropismus Zeitrafferaufnahmen von Haferkoleoptilen, die von links mit Blaulicht bestrahlt wurden. Effektiv: Blaulicht Krümmung erfolgt durch Zellstreckung auf der dem
Cornel Mülhardt. Molekularbiologie/ Genomics
 Cornel Mülhardt Molekularbiologie/ Genomics 1 Was ist denn Molekularbiologie", bitteschön? 1 1.1 Das Substrat der Molekularbiologie, oder : Molli-World für Anfänger 2 1.2 Was brauche ich zum Arbeiten?
Cornel Mülhardt Molekularbiologie/ Genomics 1 Was ist denn Molekularbiologie", bitteschön? 1 1.1 Das Substrat der Molekularbiologie, oder : Molli-World für Anfänger 2 1.2 Was brauche ich zum Arbeiten?
Seminar Biomedical Informatics
 Martin Dugas und Xiaoyi Jiang Institut für Informatik Sommersemester 2017 Organisation Vorlage: Englischsprachige Publikation Vortrag: ca. 30min + 15min Diskussion, Hand-out, Blockseminar Anfang Juni Seminararbeit:
Martin Dugas und Xiaoyi Jiang Institut für Informatik Sommersemester 2017 Organisation Vorlage: Englischsprachige Publikation Vortrag: ca. 30min + 15min Diskussion, Hand-out, Blockseminar Anfang Juni Seminararbeit:
1 Einleitung Material und Methoden... 15
 Inhaltsverzeichnis 1 Einleitung... 1 1.1 Grenzflächen höherer Pflanzen... 2 1.2 Kutin und Wachse als Bestandteile oberirdischer Grenzflächen... 2 1.3 Suberin als Bestandteil pflanzlicher Grenzflächen...
Inhaltsverzeichnis 1 Einleitung... 1 1.1 Grenzflächen höherer Pflanzen... 2 1.2 Kutin und Wachse als Bestandteile oberirdischer Grenzflächen... 2 1.3 Suberin als Bestandteil pflanzlicher Grenzflächen...
BCDS - Biochemische Datenbanken und Software
 BCDS - Biochemische Datenbanken und Software Seminarinhalte Bioinformatische Genom- und Proteomanalyse Literaturrecherche und Zitation Naturwissenschaftliche Software Termine 25. Mai, 1. Juni, 8. Juni,
BCDS - Biochemische Datenbanken und Software Seminarinhalte Bioinformatische Genom- und Proteomanalyse Literaturrecherche und Zitation Naturwissenschaftliche Software Termine 25. Mai, 1. Juni, 8. Juni,
Molecular genetic analysis of GIGANTEA
 Molecular genetic analysis of the role of GIGANTEA in flower initiation Inaugural-Dissertation zur Erlangung des Doktorgrades der Mathematisch-Naturwissenschaftlichen Fakultät der Universität zu Köln vorgelegt
Molecular genetic analysis of the role of GIGANTEA in flower initiation Inaugural-Dissertation zur Erlangung des Doktorgrades der Mathematisch-Naturwissenschaftlichen Fakultät der Universität zu Köln vorgelegt
Research Collection. Doctoral Thesis. ETH Library. Author(s): Beck, Christoph. Publication Date: 1998
 Research Collection Doctoral Thesis Die Analyse des "housekeeping"-promotors von Bradyrhizobium japonicum als Basis für die Entwicklung eines sequenzspezifischen in-vitro-transkriptionssystems Author(s):
Research Collection Doctoral Thesis Die Analyse des "housekeeping"-promotors von Bradyrhizobium japonicum als Basis für die Entwicklung eines sequenzspezifischen in-vitro-transkriptionssystems Author(s):
RNA und Expression RNA
 RNA und Expression Biochemie RNA 1) Die Transkription. 2) RNA-Typen 3) RNA Funktionen 4) RNA Prozessierung 5) RNA und Proteinexpression/Regelung 1 RNA-Typen in E. coli Vergleich RNA-DNA Sequenz 2 Die Transkriptions-Blase
RNA und Expression Biochemie RNA 1) Die Transkription. 2) RNA-Typen 3) RNA Funktionen 4) RNA Prozessierung 5) RNA und Proteinexpression/Regelung 1 RNA-Typen in E. coli Vergleich RNA-DNA Sequenz 2 Die Transkriptions-Blase
Vorlesung LV-Nr Molekularbiologie für Agrarwissenschaften. J. Glößl, SS 2007
 Vorlesung LV-Nr. 954.104 Molekularbiologie für Agrarwissenschaften J. Glößl, SS 2007 Thematik: Molekularbiologische Methoden Teil 2 Die ppt Folien wurden freundlicherweise von Prof. Florian Rüker aus der
Vorlesung LV-Nr. 954.104 Molekularbiologie für Agrarwissenschaften J. Glößl, SS 2007 Thematik: Molekularbiologische Methoden Teil 2 Die ppt Folien wurden freundlicherweise von Prof. Florian Rüker aus der
Regulation der Carotinoidbiosynthese in Nostoc PCC Dissertation Zur Erlangung des Doktorgrades der Naturwissenschaften
 Regulation der Carotinoidbiosynthese in Nostoc PCC 7120 Dissertation Zur Erlangung des Doktorgrades der Naturwissenschaften vorgelegt beim Fachbereich Biowissenschaften der Johann Wolfgang Goethe-Universität
Regulation der Carotinoidbiosynthese in Nostoc PCC 7120 Dissertation Zur Erlangung des Doktorgrades der Naturwissenschaften vorgelegt beim Fachbereich Biowissenschaften der Johann Wolfgang Goethe-Universität
- 103 ATTATATCAAGCTCCTCAATTTCACACTTTAAAAAGTTAGACTTTTCACATCTTTCATTT
 Anhang 1: Genomische Sequenz der RNase LE mit 2668 bp upstream des Translationsstartkodons gelegener Sequenz. Die Aminosäuresequenz wurde im Vergleich mit der cdna-sequenz der RNase LE (KÖCK et al., 1995)
Anhang 1: Genomische Sequenz der RNase LE mit 2668 bp upstream des Translationsstartkodons gelegener Sequenz. Die Aminosäuresequenz wurde im Vergleich mit der cdna-sequenz der RNase LE (KÖCK et al., 1995)
Sind MADS-Box-Gene ein Schlüssel zum Verständnis der Entwicklung und Evolution der Gametophyten-Generation von Landpflanzen?
 P flanzenforschung Sind MADS-Box-Gene ein Schlüssel zum Verständnis der Entwicklung und Evolution der Gametophyten-Generation von Landpflanzen? Verelst, Wim; Münster, Thomas; Max-Planck-Institut für Züchtungsforschung,
P flanzenforschung Sind MADS-Box-Gene ein Schlüssel zum Verständnis der Entwicklung und Evolution der Gametophyten-Generation von Landpflanzen? Verelst, Wim; Münster, Thomas; Max-Planck-Institut für Züchtungsforschung,
1. Welche Auswirkungen auf die Expression des lac-operons haben die folgenden Mutationen:
 Übung 10 1. Welche Auswirkungen auf die Expression des lac-operons haben die folgenden Mutationen: a. Eine Mutation, die zur Expression eines Repressors führt, der nicht mehr an den Operator binden kann.
Übung 10 1. Welche Auswirkungen auf die Expression des lac-operons haben die folgenden Mutationen: a. Eine Mutation, die zur Expression eines Repressors führt, der nicht mehr an den Operator binden kann.
Neue DNA Sequenzierungstechnologien im Überblick
 Neue DNA Sequenzierungstechnologien im Überblick Dr. Bernd Timmermann Next Generation Sequencing Core Facility Max Planck Institute for Molecular Genetics Berlin, Germany Max-Planck-Gesellschaft 80 Institute
Neue DNA Sequenzierungstechnologien im Überblick Dr. Bernd Timmermann Next Generation Sequencing Core Facility Max Planck Institute for Molecular Genetics Berlin, Germany Max-Planck-Gesellschaft 80 Institute
Michelle Kammel David Speck
 Michelle Kammel David Speck 10.07.2013 Was ist bisher bekannt? Zentrum des Signalwegs ist der Ubiquitin Ligase SCF TIR1 Komplex Gray et al. (2001) Abbau der Aux/IAA aktiviert Transkriptionsfaktoren (ARFs)
Michelle Kammel David Speck 10.07.2013 Was ist bisher bekannt? Zentrum des Signalwegs ist der Ubiquitin Ligase SCF TIR1 Komplex Gray et al. (2001) Abbau der Aux/IAA aktiviert Transkriptionsfaktoren (ARFs)
3.1 Expressionsanalyse der AtMRS2-Genfamilie
 3 Ergebnisse Über den pflanzlichen Magnesiumtransport und dessen Regulationsmechanismen ist bisher nur sehr wenig bekannt. Der bisher am besten charakterisierte Magnesiumtransporter in Arabidopsis thaliana
3 Ergebnisse Über den pflanzlichen Magnesiumtransport und dessen Regulationsmechanismen ist bisher nur sehr wenig bekannt. Der bisher am besten charakterisierte Magnesiumtransporter in Arabidopsis thaliana
