Molekularbiologie. Methoden. Dr. Thomas Seehaus
|
|
|
- Hartmut Eike Grosse
- vor 5 Jahren
- Abrufe
Transkript
1 Molekularbiologie Methoden Dr. Thomas Seehaus
2 Aufgabe Isolation des hypothetischen Gens KRYP1 aus Zucchini Seite 2
3 DNA-Extraktion aus Geweben Vorüberlegungen für einen Versuch mit Haushaltsmitteln Jede Zelle enthält im Zellkern DNA (Desoxyribonukleinsäure). Dazu kommen Proteine, Fette, Kohlenhydrate, Ionen. Um die DNA freisetzen zu können, müssen zunächst die Zellwand, Zellmembran und die Kernmembran zerstört werden. Zellwände werden mechanisch und/oder enzymatisch geöffnet. - Glasbeads, Mörsern, kalt, flüssiger Stickstoff oder Trockeneis - Enzyme Da die Membranen aus amphiphilen Molekülen aufgebaut sind, können sie mit Detergentien (in herkömmlichen Spülmitteln) aufgelöst werden. Fette werden ebenfalls im Detergenz gelöst. Die in den Spülmitteln enthaltenen Enzyme (Proteasen) zerstören außerdem begleitende Eiweiße (Proteine, u. a. DNasen!). Aufreinigung der DNA durch Ethanol-Fällung (Dehydratation der DNA => fällt aus, Kohlenhydrate und Ionen bleiben gelöst) Seite 3
4 Besonderheiten bei RNA-Extraktion RNA ist sehr viel schwieriger zu isolieren als DNA - Cytoplasma enthält sehr viele RNasen (RNA abbauende Enzyme, u. a. zur Regulation der Proteinsynthese!) - RNasen müssen inhibiert oder deaktiviert werden (Proteasen, RNaseInhibitoren, Phenol) - auf der Haut sind viele RNasen vorhanden! - Handschuhe tragen, Gerätschaften und Lösungen sterilisieren! RNA-Moleküle sind kleiner als DNA-Moleküle - Ethanol-Fällung ist daher weniger effizient - Ethanol muss sehr kalt sein (-20 C) - zur Unterstützung höherer Salzgehalt Seite 4
5 DNA-Isolierung aus Zucchini Material/Geräte: - Zucchini, (Kartoffel)reibe, Teesieb, Thermometer, 100 ml Messzylinder, zwei 100 ml Bechergläser, ein 250 ml Becherglas (niedrige Form), 60 C warmes Wasser, Spülmittel (das Proteasen enthält!), Kochsalz, Brennspiritus, Eiswürfel, evtl. kleine Styroporbox Vorbereitungen: - 20 ml Brennspiritus (oder 96 % Ethanol) eine Stunde vor dem Versuch ins Kühlfach (ca. -20 C) legen. Zum Transport auf Eis (in einer kleinen Styroporbox) legen. - Wasser (60 C) bereitstellen (z. B. in einem Babyflaschenwärmer) - Spülmittel-/Salz-Lösung zur Extraktion: 50 ml Wasser mit 5 ml Spülmittel (mit Proteasen) und 1 g Kochsalz gut mischen. Seite 5
6 DNA-Isolierung aus Zucchini - Durchführung Man reibt ein Zucchini-Stück und füllt einen Esslöffel in ein 100 ml Becherglas - Durch das Reiben wird das Pflanzengewebe zerkleinert und die Zellwände teilweise aufgebrochen und gibt 25 ml der Spülmittel-/Salz-Lösung hinzu - Das Spülmittel enthält Detergentien, die aufgrund ihrer chemischen Struktur Lipide in Lösung bringen. Salze verstärken den Effekt Seite 6
7 DNA-Isolierung aus Zucchini - Durchführung Das Becherglas für 15 Minuten in ein 60 C warmes Wasserbad stellen. Sehr gut geeignet sind dafür (gebrauchte) Babyflaschenwärmer. (Kann man bei ebay ersteigern!) - Die höhere Temperatur beschleunigt die Freisetzung der DNA und zerstört DNAsen (Enzyme, die DNA zersetzen.) In Eiswasser abkühlen. - Abkühlen verhindert DNA-Zerfall Den Zucchini-Brei durch ein Teesieb passieren. Dazu das Teesieb auf ein 250 ml Becherglas (niedrige Form) legen und mit einem Teelöffel durch das Netz streichen. Seite 7
8 DNA-Isolierung aus Zucchini - Durchführung Einen Teil (ca. 1 Teelöffel) des Breis in ein kleines Becherglas o. ä. füllen und ganz vorsichtig mit tiefgekühlten (möglichst aus der Kühltruhe) Alkohol überschichten. Dazu den Alkohol langsam seitlich hinein fließen lassen. Besser geht es mit einer Pipette. - DNA (und RNA) sind in Ethanol bei niedriger Temperatur unlöslich und fallen daher leicht aus. Die DNA wird oberhalb des Breis als weißgelbe Flocken/Klümpchen sichtbar. Durch Abgießen oder Herausfischen kann man die DNA in ein Röhrchen mit Alkohol überführen. Seite 8
9 DNA-Isolierung: Quellen Trolldenier, G.: Isolierung der Erbsubstanz aus Zucchini - die DNA-Küche (Industrieverband Agrar) Empfohlen wird auch die DNA-Extraktion aus anderen pflanzlichen Geweben, z. B. Tomaten, Kiwi, Zwiebeln usw. Interessant bleibt auch die früher häufig vorgeschlagene Extraktion aus tierischem Material z. B. Kalbsbries. Seite 9
10 Pufferlösung zur Aufbewahrung von DNA Tris-Puffer (EDTA-Tris-Acetat, ph 7.75) 10 mm (12,12 g) Tris-(hydroxy-methyl)-aminomethan 1 mm (0,74 g) Na2-EDTA (Dinatrium-Ethylendiamin-tetraacetat) mit destilliertem Wasser auf 900 ml aufgefüllt ph-wert mit 2 M Essigsäure auf 7,75 einstellen mit destilliertem Wasser auf 1000 ml Endvolumen auffüllen Aufbewahrung von DNA-Proben - in TE-Puffer bei -20 C - alternativ gefällt unter Ethanol - lyophilisiert EDTA: Komplexbildner TRIS: ph-puffer Seite 10
11 Nachweis von DNA Feulgen Nuklealreaktion (Robert J. W. F., , physiol. Chemiker, Gießen) mittels Photometrie quantitativ faßbare Färbung der DNA, der Zellkerne, Chromosomen, Plastiden, Bakterien u. Viren nach (mild-)saurer hydrolytischer Abspaltung der Purinbasen erfolgt die Umsetzung der zurückbleibenden Desoxyribose (mit freier Aldehydgruppe an C1) mit Schiff-Reagens (fuchsinschweflige Säure; 1 Std.) zu rotviolettem Farbstoff Seite 11
12 Konzentrationsbestimmung von DNA-Lösungen UV-Spektrophotometrie Nukleinsäuren besitzen ein Absorptionsmaximum bei 260 nm optische Dichte (OD260) von 1 entspricht einer Konzentration von 50 μg dsdna/ml, 35 μg RNA/ml oder 33 μg ssdna/ml. Es wird in der Regel eine 200 fache Verdünnung der Lösung in einem Endvolumen von 200 μl hergestellt und photometrisch in einer Quarzküvette gegen Wasser vermessen. Die Reinheit der DNA-Lösung kann durch das Erstellen eines Absorptionsspektrums beurteilt werden, das bei 260 nm ein Absorptionsmaximum aufweisen sollte. Verunreinigung mit Protein lassen sich durch hohe Absorption bei 280 nm identifizieren. Charakteristisch für eine saubere DNA-Lösung ist ein Wert des Quotienten 260nm/280nm nahe 2. Seite 12
13 Übersicht Enzyme für die Molekularbiologie Nukleasen - Unspezifische Nukleasen (Endo- und Exonukleasen, Dnase, RNase) - Spezifische Endonukleasen (Restriktions-Endonukleasen) Ligasen Polymerasen - DNA-abhängige DNA-Polymerasen (Replikation) - RNA-abhängige DNA-Polymerasen (Reverse Transkription) - DNA-abhängige RNA-Polymerasen (Transkription) Kinasen Phosphatasen Seite 13
14 Isolierte DNA handlich machen Unsere isolierte DNA besteht idealerweise aus Zucchini-Chromatiden (Länge mehrere cm/dm pro Molekül!) - DNA-Moleküle können brechen/zerreißen - gesuchtes Gen irgendwo auf den Chromatiden versteckt - übliche Trennmethoden mit so langen DNAMolekülen überfordert Aufgabe: - reproduzierbare Zerlegung der DNA in handliche Fragmente Welche Methoden stehen zur Verfügung? Seite 14
15 Unspezifische Nukleasen Exonuclease III Exonuklease - dsdna mit einem Einzelstrangbruch - mit blunt ends - 3 recessed ends Nuklease Bal 31 (Alteromonas expejiana) - dsdna => 3 - und 5 -Exonuklease - ssdna => Endonuklease - Ca-abhängige Reaktionen, Stop durch EDTA - Gezielte Verkürzung von DNA Nuklease S1 (Aspergillus oryzae) - ssdna => Endonuclease (ph<4,5 / T<20 C!) - Abbau ungepaarter Bereiche in DNA-RNAHybriden (cdna-synthese) Seite 15
16 Unspezifische Nukleasen DNase I (Rinder-Pankreas) - dsdna und ssdna, zufälliges Schneiden beider Stränge - Entfernen von DNA, Einführen statistischer Schnittstellen in einzelne Stränge - Enzym besitzt 3 verschiedene Aktivitäten, die in gentechnischen Experimenten unterschiedlich genutzt werden können Polymerase-Aktivität : freie 3 OH-Enden, freie Nukleotide, Mg2+ als Kofaktor, Einzelstrangmatritze Exonuklease-Aktivität: Abbau von DNA im Doppelstrang (Reparatur) Exonuklease-Aktivität: Korrekturlesen (in Gegenwart von dntp s gehemmt) - Polymerase-und Exonuklease-Aktivitäten liegen im intakten Enzym im Gleichgewicht vor - Polymerasefunktion kann durch Salzkonzentration und die Konzentration freier Nukleotide erhöht werden Seite 16
17 λ-phagen infizieren E. coli unterschiedlich effizient! Paar von Enzymen schützt Bakterien Methylase markiert eigene DNA an spezifischen Stellen Endonuklease schneidet DNA an den spezifischen Stellen, wenn diese nicht methyliert sind => fremde DNA wird abgebaut! Seite 17
18 Spezifische Nukleasen (Restriktionsenzyme) Quelle: Bakterien - Restriktion: Immunität gegen Phagen, Schutz vor fremder DNA - Schutz der eigenen DNA durch spezifische Methylierungsmuster Als Werkzeuge interessant: - Typ II Endonukleasen (sequenzspezifische Bindung und Hydrolyse) Erkennungssequenzen: - Palindrome / Nicht-Palindrome Basenpaare (4-, 5-, 6-, 8- cutter) Isochizomere: Gleiche ES, gleiche Schnittstelle Neochizomere: Gleiche ES, andere Schnittstelle Schnitt-Frequenzen (statistisch!): - 4-cutter = 1/256 bp, 6-cutter = 1/4096 bp, 8-cutter = 1/65536 bp Entstehende Fragmente: 5 -Phosphat, 3 -OH Seite 18
19 Restriktions-Enzyme Typ I: Schneidet die DNA an einer zufälligen Stelle weit von der Erkennungssequenz entfernt. Benötigt ATP und transferiert eine Methylgruppe von S-Adenosyl-Methionin. Typ II: Schneidet die DNA innerhalb der Erkennungssequenz. Benötigt kein ATP und hat keine Methyltransferase-Aktivität. Typ III: Schneidet die DNA etwa 20 bis 25 Basenpaare von der Erkennungssequenz entfernt. Benötigt ATP und transferiert eine Methylgruppe von S-Adenosyl-Methionin. Beispiele für Typ II: Seite 19
20 Restriktion genomischer DNA vollständige Restriktion mit einer Restriktionsendonuklease vollständige Restriktion mit zwei verschiedenen Restriktionsendonukleasen partielle Restriktion mit einer Restriktionsendonuklease Seite 20
21 Auftrennen von DNA-Fragmenten Agarose-Gel zur Trennung verschieden langer DNA-Fragmente Trennende Kraft: elektrische Spannung negativ geladene DNA wandert von der Anode zur Kathode poröse Gelstruktur setzt der Wanderung der Fragmente Widerstand entgegen je kleiner die Fragmente sind, desto schneller wandern sie Seite 21
22 Wiedergewinnung von DNA aus Agarose-Gel Achtung: UV-Licht schädigt die Augen! Ethidium Bromid interkaliert in dsdna Nachweis der DNA durch Fluororeszenz Gelstückchen können ausgeschnitten und die DNA eluiert werden Wiedergewinnung der DNA durch Ethanolfällung Seite 22
23 Verbinden von DNA-Fragmenten kompatible Enden von RestriktionsFragmente hybridisieren miteinander dsdna wird gebildet DNA-Ligase schließt Lücken im ZuckerPhosphat-Rückgrad der DNA Doppelhelix aus zwei verschiedenen DNAs hergestellt Seite 23
24 DNA-Ligasen Verknüpfung des 3 -OH eines DNA-Fragments mit dem 5 -Phosphat eines anderen benötigt ATP Häufigste: T4-Ligase Komplementäre sticky ends - Raumtemperatur - Reaktionszeit einige Stunden Blunt ends - 10 C oder Kühlschrank - Reaktionszeit über Nacht - Effizienz gering, da keine stabilisierenden Wasserstoffbrücken zwischen den zu verbindenden DNA-Fragmenten Seite 24
25 Ligation verschiedener Restriktionsfragmente Seite 25
26 Ligationsstrategien Seite 26
27 Plasmide ringförmige, extrachromosomal lokalisierte DNA-Moleküle, die in den meisten gram-positiven und gram-negativen Bakterien, in einigen Hefen, aber nicht in höheren Eukaryoten vorkommen wurden Anfang der 50-er Jahre durch das Auftreten und die schnelle Ausbreitung von Antibiotika-Resistenzen entdeckt verschaffen den Wirtszellen in entsprechender Umgebung (Anwesenheit des Antibiotikums) einen Wachstumsvorteil Unterscheidung von konjugativen (F-Plasmid) und nicht-konjugativen Plasmiden konjugative Plasmide können durch Transfer von einer Donorzelle in eine Rezipientenzelle übertragen werden (Konjugation) Verwendung von nicht-konjugativen Plasmiden in der Gentechnik (biologische Sicherheit) Seite 27
28 Eigenschaften von Vektoren Replikationsursprung - Voraussetzung für die Replikation selektierbare Marker - Nachweis der Anwesenheit des Plasmids in Bakterienzellen - Antibiotikaresistenz - auxotrophe Marker Restriktionsschnittstellen - nur je eine für verschiedene RestriktionsEndonukleasen, jedoch innerhalb der Marker, zur Linearisierung geringe Größe idealerweise bekannte DNA-Sequenz Seite 28
29 Verknüpfung von DNA-Fragmenten T4 Ligase als meist genutztes Enzym für die Verknüpfungsreaktion Abhängigkeit der Verknüpfungsreaktion von der Konzentration der DNAFragmente Bevorzugung von inter- oder intramolekularer Reaktion ist von der DNAKonzentration und der Fragmentgröße abhängig konstante DNA-Konzentration Größe des DNA-Fragmentes Neigung zur intramolekularen Reaktion konstante DNA-Fragmentlänge DNA-Konzentration Neigung zur intramolekularen Reaktion hohe DNA-Konzentrationen Bevorzugung intermolekularer Reaktion bei Klonierungsexperimenten ist bevorzugt eine bimolekulare Reaktion erwünscht Seite 29
30 optimale Konzentrationen für bimolekulare Reaktion Seite 30
31 Prinzip der DNA-Klonierung Linearisierung des Vektors und der Fremd-DNA mit gleicher oder kompatibler Restriktions-endonuklease Mischen der beiden DNAs in optimaler Konzentration Ligierung mit T4-DNALigase Transformation in kompatible Wirtszellen (meist E.coli) Seite 31
32 Transformation einige Bakterien besitzen die Eigenschaft DNA aus der Umgebung aufnehmen zu können Labormethoden zur Erhöhung der Aufnahmeeffizenz: Hitzeschock - Bakterienzellen werden mit Calciumchlorid oder effektiver mit Rubidiumchlorid behandelt, so dass zwischen der negativ geladenen DNA und der negativ geladenen Zellmembran weniger abstoßende Kräfte bestehen. Bei einem kurzen Hitzeschock (41 43 C für Sekunden) entstehen Poren in der Membranen, so dass die DNA in die Zellen gelangen kann. Elektroporation - Hierbei werden die Bakterien mit einem elektrischen Schock behandelt ( V für einige Millisekunden), um die Membran zu öffnen. Diese Methode ist effektiver als die chemische Methode Anschließend Kultur unter Selektionsbedingungen Seite 32
33 Selektion der gesuchten Plasmide Mögliche Ligationsergebnisse: 1.Vektor religiert 2.Fremd-DNA religiert 3.Vektor + Fremd-DNA ligiert Gesucht: keine Replikation in Bakterien (ORI fehlt) Bei Klonierung in BamH1-Stelle: - 1. Klone Ampicillin- und Tetrazyklin resistent - 3. Klone nur Ampicillin resistent Identifikation der Klone durch Stempeln auf Ampicillin- und Tetrazyklin-Platten Seite 33
34 Replikaplattierung Seite 34
35 Selektionsbeispiel Seite 35
36 Kinasen / Phosphatasen Kinasen - Anhängen eines Phosphats an 5 -OH einer Nukleinsäure - unter Verbrauch von ATP - Häufigste: T4-Polynucleotidkinase - Anwendung: - Markierung mit radioaktivem 32P - Auffüllen dephosphorylierter 5'-Enden Phosphatasen - Abspalten eines Phosphats vom 5 -Ende einer Nukleinsäure - BAP (Bacterial Alkaline Phosphatase) - CIP (Calf Intestine Phosphatase) - Anwendung: Verhinderung unerwünschter Ligation Seite 36
37 Verhinderung der Vektor-Religierung Alkalische Phosphatase entfernt 5'-Phosphat linearisierter Vektor kann nicht mehr rezyklisiert werden Bei Hybriden mit Fremd-DNA kann zumindest je Strang eine Lücke geschlossen werden Seite 37
38 Nachweis bestimmter DNA-Sequenzen Nach der Klonierung unseres Gemisches von DNA-Fragmenten aus Zucchini erhalten wir eine Fülle von Klonen, von denen einige wenige das oder die gesuchten Fragmente enthalten sollten Wie können wir diese identifizieren? einige Möglichkeiten: - Komplementation auxotropher Mutanten (Mangelmutanten) - Fragment muss intaktes Gen enthalten, das auxotrophe Mutation komplementieren kann - Zielorganismus (E.coli) muss Gen des Spenders (Zucchini) verstehen - Vektor muss zur Genexpression (Transkriptions-Signale) fähig sein - Direkte Identifikation durch DNA-DNA-Hybridisierung mit Sonden-DNA - Sequenz muss zumindest teilweise bekannt sein, z. B. Ableitung aus Proteinsequenz, bekannte Sequenz eines nahe verwandten Organismus - Sonde muss markiert sein Seite 38
39 DNA-Polymerasen DNA-Polymerase I aus E. coli (Kornberg-Polymerase) - DNA-Synthese 5 =>3 an DNA-Matrize und Primer Exonuklease Exonuklease - Nick-Translation Klenow-Polymerase - Proteolyse der DNA-Polymerase I - Klenow-Fragment => stark verminderte Exonuklease - Auffüllen von Einzelsträngen, benötigt Primer Thermostabile DNA-Polymerasen - PCR-Enzyme! Seite 39
40 nick translation A) DNase I erzeugt Einzelstrang-Brüche (nicks) indem sie die PhosphodiesterBindungen (p) spaltet. Dabei entsteht eine 5'-Phosphat-Gruppe und ein 3'-HydroxylEnde. Zugabe von E. coli DNA Polymerase I liefert zwei Enzymaktivitäten: i. 5' 3' Exonuclease entfernt vom freien 5'-Ende sequentiell Nukleotide in 5' 3' Richtung ii. DNA Polymerase baut von der freien 3'Hydroxyl Gruppe in 5' 3' Richtung neue Nukleotide ein und füllt die, durch Exonuklease erzeugte, Lücke wieder auf (translation) B) Random primed labeling. KlenowPolymerase synthetisiert radioaktiv markierte DNA-Stränge anhand hitzedenaturierter Einzelstrang-Matritzen mit Hexanukleotid Primern mit zufälligen Sequenzen Seite 40
41 End-Markierung von DNA A) Markierung von Oligonukleotiden durch Kinase. Das 5'-terminale Phosphat wird in einer Austauschreaktion durch 32P-markiertes Phosphate aus [ -32P]-ATP ersetzt. Auf gleiche Weise können beide 5'-Enden doppel-strängiger DNA markiert werden. B) Auffüllen überhängender Enden mit KlenowPolymerase. DNA wird mit einer passenden Restriktions Endonuclease gepalten um 5'-Überhänge zu erzeugen. Diese dienen als Primer für Klenow_Polymerase um markierte Nukleotide ein zu bauen. Fragmente, die nur an einem Ende markiert sind, können durch internes Schneiden in einer passenden Restriktionsstelle erzeugt werden, um zwei unterschiedlich große Fragments zu erhalten, die leicht nach der Größe fraktioniert werden können. Seite 41
42 Markierungsmöglichkeiten für DNA radioaktiv: - 32 P ([ -32P]ATP) - 35 S (ersetzt O- in [ -P]ATP) - Nachweis durch Autoradiographie (Schwärzung eine Films durch radioaktive Substanzen) nicht radioaktiv - Fluoreszierende Gruppe - anitgene Gruppe (Digoxigenin, Nachweis mit anti-digoxigeninantikörper, der an Reportermolekül gekoppelt ist, das wiederum Farbreaktion auslöst) -... Seite 42
43 Hybridisierung Seite 43
44 Hybridisierung und Renaturierung Seite 44
45 Southern Transfer Seite 45
46 Hybridiserung und Autoradiografie Seite 46
47 Southern - Ergebnisse Seite 47
48 RFLPs: Restriction Fragments Length Polymorphisms verschiedene Allele eines Gens können verschiedene Restriktionsmuster produzieren diese Muster sind vererbbar Verwendung: - Genomkartierung Analyse von Varianten Verwandschaftsanalyse DNA-Fingerprinting Seite 48
49 DNA - fingerprinting D2: Tochter aus erster Ehe der Mutter S2: Adoptivsohn DNA des Verdächtigen 1 stimmt mit Sperma-DNA vom Tatort überein boyfriend war nicht beteiligt Seite 49
50 Übersicht Blotting - Methoden Prinzip - Trennung von Makromolekülen durch Elektrophorese - Transfer der Moleküle aus dem Gel auf Nitrozellulosemembran - Nachweis spezifischer Moleküle Southern - Makromoleküle: DNA - Nachweis: Hyridisierung mit markierten Sonden (DNA, Oligonukleotide) Northern - Makromoleküle: RNA - Nachweis: Hyridisierung mit markierten Sonden (DNA, Oligonukleotide) Western - Makromoleküle: Proteine - Nachweise: Antikörper Seite 50
51 Verschiedene Vektortypen Vektor Plasm id Bacteriophage Cosmids BACs (künstliche Bakterienchromosomen) YACS (künstliche Hefechromosomen) Einbaugröße (kb) <10 kb 9-20 kb kb kb kb Cosm ide sind Plasm id-vektoren, die cos-sequenzen (Phage λ) enthalten. Diese sind für die Integration in Phagen notwendig Expressionsvektoren - klonierte DNA soll in Wirtszellen exprimiert werden - Probleme: - Wirtszelle muss DNA-Regulation des Ausgangsorganismus verstehen - gesamte Regulationseinheit muss kloniert sein - Lösung: Klonierung des prozessierten Gens: mrna Seite 51
52 Klonierung von prozessierten Genen: cdna Isolation von mrna - Regulation hat stattgefunden - Splicing hat stattgefunden - endgültige kodierende Sequenz - Polyadenylierung durchgeführt DNA-Synthese - poly-dt als Primer! - Reverse Transkriptase als DNAPolymerase zweite Syntheserunde zur Produktion von dsdna Klonierung der fertigen Gene in Expressionsvektoren Seite 52
53 RNA-abhängige DNA-Polymerasen Reverse Transkriptasen - Umschreibung retrovorale RNA in DNA - Laboranwendung: cdna-synthese aus RNA Enzme: AMV-RT (Avian Myeloblastosis Virus) - RNase H, (DNA-abh. DNA-Pol.) - T = 42 C, niedrigere Prozessivität (1-2 kb) MMLV-RT (Moloney Mouse Leukemia Virus) - geringere RNase H - T = 37 C, höhere Prozessivität (> 2 kb) Modifizierte MMLV-RT (SuperScript etc.) - keine RNase H! - Produktlängen bis 20 kb! Seite 53
54 Primer Oligo-dT-Primer dt - Hybridisierung mit 3 -PolyA-Schwanz der mrna - Möglichkeit der Full-length-cDNA Random-Primer - Statistische Hexamere - Alle Bereiche von mrna und Nicht-mRNA vertreten Spezifische Primer - Bei bekannter Sequenz - Niedrige Ausbeuten Anwendungen: - cdna-banken - RT-PCR Seite 54
55 DNA-abhängige RNA-Polymerasen Enzyme der regulären Transkription Verwendung als Werkzeuge: Polymerasen aus Phagen - SP6-Polymerase - T3-Polymerase - T7-Polymerase Erkennung spezifischer Promotor-Sequenzen RNA-Synthese 3 von diesen Sequenzen Seite 55
56 DNA-Bibliotheken Quelle: - genomische DNA - cdna Ziel: - möglichst jede DNA-Sequenz eines Organismus in Plasmid kloniert (Genomsequenzierung) - möglichst jede mrna eines Organismus als Klon (Physiologie, Zellzyklus, etc) Seite 56
57 Expression humaner Antikörper in Bakterien Klonierung des Vektors psex in E.coli führt zu Produktion veränderter M13-Phagen Ein Teil der Bindeprotein piii trägt eine humane erste Antikörperdomäne mit Antigenbindestelle Seite 57
58 DNA-Bibiliothek in YACs Mit Hilfe dieser Methode können extrem lange DNA-Fragmente bis zu 1 MBb (z. B. zur Erzeugung von Genombibliotheken) kloniert werden Erzeugung langer Fragmente durch partiellen Restriktionsverdau Es können Regulationsmechanismen größerer Geneinheiten untersucht werden Seite 58
59 Expression in Pflanzen Agrobacterium tumefaciens (erzeugt Tumore in den Wirtspflanzen) Bei der Infektion einer Pflanze durch das Bakterium verlässt ein Stück DNA (= T-DNA) mit 30,000 Basenpaaren das Plasmid und integriert sich in die DNA der pflanzlichen Wirtszelle. Die Tumorgene der T- DNA müssen inaktiviert werden Fremdgene müssen an dieselbe Stelle des TiPlasmids integriert werden. Das rekombinante Plasmid mit dem integrierten Gen muß dann wieder in die A. tumefaciens Zelle transferiert werden. Die Bakterienzelle muß nun in das Protoplasma der Pflanzenzelle gebracht werden. Die Wirtspflanzen exprimieren die eingebarchten Gene Seite 59
60 Transgene Pflanzen: einige Beispiele Anti-Matsch-Tomate Transgene Sojapflanzen Polygalacturonase (PG) Resistenz gegen Roundup, Liberty Bt-Mais ( Genmais ) Seite 60
61 Polymerase Kettenreaktion PCR Seite 61
62 Molekularbiologie Methoden Polymerase-Kettenreaktion (PCR) Dr. Thomas Seehaus
63 Geschichte 1970 Kjell Kleppe: Vermehrung von DNA durch zwei flankierende Primer, wegen fehlender technischer Möglichkeiten geriet die Methode wieder in Vergessenheit 1983 Kary Banks Mullis: erneute Erfindung der PolymeraseKettenreaktion, Idee: künstliche Vervielfältigung von DNA durch wiederholte Verdopplung in mehreren Zyklen mit Hilfe von DNAPolymerase Verbesserung: Verwendung von thermostabilen DNA-Polymerasen aus thermophilen Bakterien Taq-Polymerase aus Thermus aquaticus, fehleranfällig -> Mutationen! Pwu-Polymerase aus Pyrococcus woesei, Korrekturmechanismus! Pfu-Polymerase aus Pyrococcus furiosus, ebenfalls Korrekturmechanismus Seite 63
64 PCR in der Praxis Vervielfältigung von kurzen (bis 3000 bp), genau definierten Teilen eines DNA-Stranges Benötigte Komponenten: - Original-DNA - zwei Primer, die den zu vermehrenden Bereich berenzen - thermostabile Polymerase - Nukleotide - Mg2+-Ionen (Kofaktor der Polymerasen) - Pufferlösungen (geeignete chemische Umgebung für Polymerasen) - Thermocycler Seite 64
65 PCR - Beispiel 1,0 µl DNA-Vorlage (100 ng/µl) 2,0 µl pro Primer (10 µm) 1,0 µl Pfu-, Taq- oder andere thermostabile Polymerase (1-5 U/µl) 1,0 µl 10 mm Desoxy-Nukleotide (datp, dgtp, dctp, dttp), dntp 5,0 µl 10fach konzentrierte Polymerase-Pufferlösung 38,0 µl H2O ad 50,0 µl Gesamtvolumen Ein 200 µl-reaktionsgefäß mit den 50 µl Gemisch wird in den Thermocycler gestellt. Seite 65
66 Ablaufschema der PCR (1) Schmelzen (Denaturierung) bei ca. 96 C. (2) Anlagerung (Primerhybridisierung) bei ca. 68 C. (3) Verlängerung (Elongation) bei ca. 72 C (P=Polymerase). (4) Der erste Zyklus ist beendet. Seite 66
67 Schritte des PCR-Prozesses Die folgenden Angaben sind als Richtwerte gedacht. Meist muss eine PCR auf die spezifische Reaktion hin optimiert werden. Für eine normale Präparation eines Amplifikats reicht folgendes Programm aber aus: Initialisierung. Das Gemisch wird ca. 2 Minuten lang auf 96 C erhitzt, um sicherzustellen, dass sich die DNA-Doppelstränge getrennt haben. Manche (sogenannte hot start-) Polymerasen müssen auch durch eine noch längere anfängliche Erhitzungs-Phase (bis zu 15 Minuten) erst aktiviert werden. Denaturierung. Die Temperatur ca. 30 Sekunden lang auf 96 C halten. Das genügt gewöhnlich, um die DNA während der Zyklen zu zerlegen. Anlagerung (annealing). Die Temperatur ca. 30 Sekunden lang auf einer Temperatur halten, die eine spezifische Anlagerung der Primer an die DNA erlaubt. Die genaue Temperatur wird hierbei durch die Länge und die Sequenz der Primer bestimmt (bzw. der passenden Nukleotide im Primer, wenn durch diesen Mutationen eingeführt werden sollen = site-directed Mutagenesis). Wird die Temperatur zu niedrig gewählt, können sich die Primer u. U. auch an nicht 100%komplementären Sequenzen anlagern und so zu unspezifischen Produkten ( Geisterbanden ) führen. Wird die Temperatur zu hoch gewählt, ist die thermische Bewegung der Primer u. U. so gross, dass sie sich nicht richtig anheften können, so dass es zu gar keiner oder nur ineffizienter Produktbildung kommt. Meist liegt die Temperatur bei 55 C bis 65 C. Seite 67
68 Schritte des PCR-Prozesses Verlängerung (elongation). Die Temperatur für ca. 30 Sekunden je 500 Basenpaare auf C (je nach Polymerase) halten. Die Schritte 2-4 werden mal wiederholt. Das Gemisch wird bei 4-8 C aufbewahrt. Man kann die PCR am Abend vor dem Verlassen des Labors einleiten, so dass sie über Nacht läuft. Die DNA wird bei 4-8 C nach nur einer Nacht nicht beschädigt. Das PCR-Produkt kann durch Agarose-Gelelektrophorese anhand seiner Größe identifiziert werden. (Die Agarose-Gelelektrophorese ist ein Verfahren, bei der DNA in ein Agarose-Gel eingebracht wird und anschließend eine Spannung angelegt wird. Dann bewegen sich die kürzeren DNA-Stränge schneller als die längeren auf den Pluspol zu.) Die Menge des PCR-Produkts kann durch einen Vergleich mit einer DNA-Leiter, die DNA-Fragmente bekannter Größe enthält und parallel zur Probe im Gel mitläuft, bestimmt werden. Das PCR-Produkt in niedriger (Bande 2) und hoher (Bande 3) Konzentration im Vergleich mit der DNA-Leiter (Bande 1) in Agarose-Gel. Seite 68
Bioinformatik I: Grundlagen der Gentechnik
 Bioinformatik I: Grundlagen der Gentechnik Dr. Maik Böhmer Institut für Biologie und Biotechnologie der Pflanzen Schlossplatz 7 Schwerpunkte: Vorlesung 1: Einführung & Enzyme der Gentechnik Vorlesung 2:
Bioinformatik I: Grundlagen der Gentechnik Dr. Maik Böhmer Institut für Biologie und Biotechnologie der Pflanzen Schlossplatz 7 Schwerpunkte: Vorlesung 1: Einführung & Enzyme der Gentechnik Vorlesung 2:
Restriktion und Gentechnik
 Restriktion und Gentechnik Einteilung 1.) Restriktion - Restriktionsenzyme - Southern Blotting 2.)Gentechnik - sticky ends - blunt ends Restriktion Grundwerkzeuge der Gentechnik - Restriktionsenzymanalyse
Restriktion und Gentechnik Einteilung 1.) Restriktion - Restriktionsenzyme - Southern Blotting 2.)Gentechnik - sticky ends - blunt ends Restriktion Grundwerkzeuge der Gentechnik - Restriktionsenzymanalyse
Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR)
 PCR Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR) von Kary B. Mullis entwickelt (1985) eigentlich im Mai 1983 bei einer nächtlichen Autofahrt erstes erfolgreiches Experiment am 16.12.1983
PCR Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR) von Kary B. Mullis entwickelt (1985) eigentlich im Mai 1983 bei einer nächtlichen Autofahrt erstes erfolgreiches Experiment am 16.12.1983
Antibiotika sind oft Inhibitoren der Genexpression
 Antibiotika sind oft Inhibitoren der Genexpression Inhibitoren der Transkription: Rifampicin, Actinomycin α-amanitin Inhibitoren der Translation: Puromycin, Streptomycin, Tetracycline, Chloramphenicol
Antibiotika sind oft Inhibitoren der Genexpression Inhibitoren der Transkription: Rifampicin, Actinomycin α-amanitin Inhibitoren der Translation: Puromycin, Streptomycin, Tetracycline, Chloramphenicol
Genetik Praktikumsklausur SS2005
 Genetik Praktikumsklausur SS2005 1. Aufgabe: Der Genotyp AbaB wird geselbstet, dabei werden 256 Nachkommen gebildet. Davon erhalten 16 Pflanzen den Genotyp ABAB a) gekoppelt b) nicht gekoppelt c) teilweise
Genetik Praktikumsklausur SS2005 1. Aufgabe: Der Genotyp AbaB wird geselbstet, dabei werden 256 Nachkommen gebildet. Davon erhalten 16 Pflanzen den Genotyp ABAB a) gekoppelt b) nicht gekoppelt c) teilweise
5 NUKLEINSÄUREN. In diesem Versuch wird ein kommerzielles Plasmid (plitmus38, Firma: NEB, siehe Abbildung) eingesetzt.
 5 NUKLEINSÄUREN Nukleinsäuren sind Polynukleotide, wobei jedes Nukleotid sich aus einem Phosphat, einer Ribose (RNA) oder Desoxyribose (DNA) und einer Purin- oder Pyrimidin-Base zusammensetzt. Die einzelnen
5 NUKLEINSÄUREN Nukleinsäuren sind Polynukleotide, wobei jedes Nukleotid sich aus einem Phosphat, einer Ribose (RNA) oder Desoxyribose (DNA) und einer Purin- oder Pyrimidin-Base zusammensetzt. Die einzelnen
MODULE für den SCHULKOFFER GENTECHNIK
 MODULE für den SCHULKOFFER GENTECHNIK Modul 1 - DNA-Bastel-Set Zusammenbau eines Papiermodells in Form einer Doppelhelix sehr einfach, Unterstufe, ohne Koffer möglich Modul 2 - DNA-Isolierung aus Gemüse
MODULE für den SCHULKOFFER GENTECHNIK Modul 1 - DNA-Bastel-Set Zusammenbau eines Papiermodells in Form einer Doppelhelix sehr einfach, Unterstufe, ohne Koffer möglich Modul 2 - DNA-Isolierung aus Gemüse
Bioinformatik I: Grundlagen der Gentechnik/Genomik
 Bioinformatik I: Grundlagen der Gentechnik/Genomik Prof. Dr. Antje von Schaewen (10.12. und 14.01) schaewen@uni-muenster.de Vertretung von Prof. Jörg Kudla (Freisemester) Institut für Biologie und Biotechnologie
Bioinformatik I: Grundlagen der Gentechnik/Genomik Prof. Dr. Antje von Schaewen (10.12. und 14.01) schaewen@uni-muenster.de Vertretung von Prof. Jörg Kudla (Freisemester) Institut für Biologie und Biotechnologie
Cornel Mülhardt. Molekularbiologie/ Genomics
 Cornel Mülhardt Molekularbiologie/ Genomics 1 Was ist denn Molekularbiologie", bitteschön? 1 1.1 Das Substrat der Molekularbiologie, oder : Molli-World für Anfänger 2 1.2 Was brauche ich zum Arbeiten?
Cornel Mülhardt Molekularbiologie/ Genomics 1 Was ist denn Molekularbiologie", bitteschön? 1 1.1 Das Substrat der Molekularbiologie, oder : Molli-World für Anfänger 2 1.2 Was brauche ich zum Arbeiten?
GEIM- TECHIMOLOGISCHE ARBEITSMETHODEN
 GEIM- TECHIMOLOGISCHE ARBEITSMETHODEN Ein Handbuch experimenteller Techniken und Verfahren Herausgegeben von Rudolf Hagemann Bearbeitet von Frank Baldauf, Jörn Belter, Sabine Brantl, Baimund Eck, Karsten
GEIM- TECHIMOLOGISCHE ARBEITSMETHODEN Ein Handbuch experimenteller Techniken und Verfahren Herausgegeben von Rudolf Hagemann Bearbeitet von Frank Baldauf, Jörn Belter, Sabine Brantl, Baimund Eck, Karsten
DNA-Analytik. Beispiel: Nachweis von gentechnisch veränderten Lebensmitteln
 DNA-Analytik Beispiel: Nachweis von gentechnisch veränderten Lebensmitteln rdna PCR mrna RT-PCR Protein (Enzym) Immunochemie Produkt Stoffanalytik 1. Extraktion der DNA aus den Lebensmitteln 2. DNA liegt
DNA-Analytik Beispiel: Nachweis von gentechnisch veränderten Lebensmitteln rdna PCR mrna RT-PCR Protein (Enzym) Immunochemie Produkt Stoffanalytik 1. Extraktion der DNA aus den Lebensmitteln 2. DNA liegt
Seminarbericht Jugendakademie Mannheim
 Seminarbericht Jugendakademie Mannheim Stiftung Begabtenförderung der Stadt Mannheim Oberstufe 2014/2015 Seminarthema: Biotechnologisches Praktikum Ort: BASF Agrarzentrum Limburgerhof BASF Ludwigshafen
Seminarbericht Jugendakademie Mannheim Stiftung Begabtenförderung der Stadt Mannheim Oberstufe 2014/2015 Seminarthema: Biotechnologisches Praktikum Ort: BASF Agrarzentrum Limburgerhof BASF Ludwigshafen
AUFGABENSAMMLUNG. Restriktionsenzyme. Füllen Sie den Lückentext aus. Gentechnik Schroedel, Braunschweig
 Restriktionsenzyme Füllen Sie den Lückentext aus. PCR 1a Mit dem folgenden Quiz können Sie Ihr Wissen zum Thema PCR überprüfen. Klicken Sie jeweils die richtige Antwort an. PCR 1b Mit dem folgenden Quiz
Restriktionsenzyme Füllen Sie den Lückentext aus. PCR 1a Mit dem folgenden Quiz können Sie Ihr Wissen zum Thema PCR überprüfen. Klicken Sie jeweils die richtige Antwort an. PCR 1b Mit dem folgenden Quiz
In situ Hybridisierung
 In situ Hybridisierung eine Methode zum direkten und spezifischen Nachweis von Nukleinsäuren (DNA und RNA) in Gewebe, Zellen, Zellkompartimenten und Chromosomen Was kann damit erreicht werden? direkte
In situ Hybridisierung eine Methode zum direkten und spezifischen Nachweis von Nukleinsäuren (DNA und RNA) in Gewebe, Zellen, Zellkompartimenten und Chromosomen Was kann damit erreicht werden? direkte
SCRIPTUM HIGH PRECISE
 Nur für Forschungszwecke Datenblatt Artikel BS.50.020 = 20 Reaktionen x 50 µl Artikel BS.50.100 = 100 Reaktionen x 50 µl Artikel BS.50. 500 = 500 Reaktionen x 50 µl Haltbarkeit: 12 Monate Lagerung bei
Nur für Forschungszwecke Datenblatt Artikel BS.50.020 = 20 Reaktionen x 50 µl Artikel BS.50.100 = 100 Reaktionen x 50 µl Artikel BS.50. 500 = 500 Reaktionen x 50 µl Haltbarkeit: 12 Monate Lagerung bei
Gentechnische Methoden
 Desmond S. T. Nicholl Gentechnische Methoden 2. Auflage Aus dem Englischen übersetzt von Renate FitzRoy und Kurt Beginnen Spektrum Akademischer Verlag Heidelberg Berlin Inhalt Vorwort XI 1. 1.1 1.2 1.3
Desmond S. T. Nicholl Gentechnische Methoden 2. Auflage Aus dem Englischen übersetzt von Renate FitzRoy und Kurt Beginnen Spektrum Akademischer Verlag Heidelberg Berlin Inhalt Vorwort XI 1. 1.1 1.2 1.3
Vorlesung LV-Nr Molekularbiologie für Agrarwissenschaften. J. Glößl, SS 2007
 Vorlesung LV-Nr. 954.104 Molekularbiologie für Agrarwissenschaften J. Glößl, SS 2007 Thematik: Molekularbiologische Methoden Teil 2 Die ppt Folien wurden freundlicherweise von Prof. Florian Rüker aus der
Vorlesung LV-Nr. 954.104 Molekularbiologie für Agrarwissenschaften J. Glößl, SS 2007 Thematik: Molekularbiologische Methoden Teil 2 Die ppt Folien wurden freundlicherweise von Prof. Florian Rüker aus der
Biochemisches Grundpraktikum
 Biochemisches Grundpraktikum Dr. Ellen Hornung; Email: ehornun@gwdg.de; Tel: 39-5748 Einteilung der Praktikumsplätze: Eintragen in Listen am - Dienstag, 10.11.2009, von 12:00 13:00 - Freitag, 13.11.2009,
Biochemisches Grundpraktikum Dr. Ellen Hornung; Email: ehornun@gwdg.de; Tel: 39-5748 Einteilung der Praktikumsplätze: Eintragen in Listen am - Dienstag, 10.11.2009, von 12:00 13:00 - Freitag, 13.11.2009,
Modifizierte Gene Editor Mutagenese
 Modifizierte Gene Editor Mutagenese zur gleichzeitigen Einführung mehrerer Punktmutationen DNA Template Präparation: 2 µg Plasmid DNA (bei 6 kb, sonst entsprechend mehr oder weniger) + 2 µl 2M NaOH, 2
Modifizierte Gene Editor Mutagenese zur gleichzeitigen Einführung mehrerer Punktmutationen DNA Template Präparation: 2 µg Plasmid DNA (bei 6 kb, sonst entsprechend mehr oder weniger) + 2 µl 2M NaOH, 2
Während der Synthese synthetisiert die Polymerase den neuen Strang in 5 3 Richtung und bewegt sich in 3 5 -Richtung am Matrizenstrang entlang:
 4.4 Replikation und PCR Ablauf der Replikation in vivo: Die Replikation wird von einer DNA-abhängigen DNA- Polymerase katalysiert. Jede DNA-Polymerase synthetisiert den neuen Strang in 5 3 Richtung, hierzu
4.4 Replikation und PCR Ablauf der Replikation in vivo: Die Replikation wird von einer DNA-abhängigen DNA- Polymerase katalysiert. Jede DNA-Polymerase synthetisiert den neuen Strang in 5 3 Richtung, hierzu
GENTECHNIK BEI PFLANZEN
 - 1 - GENTECHNIK BEI PFLANZEN 1. Grüne Gentechnik - was ist das? "Grüne Gentechnik" ist laut Gentechnik-Wörterbuch eine "umgangssprachliche Bezeichnung für gentechnische Forschung mit Pflanzen, während
- 1 - GENTECHNIK BEI PFLANZEN 1. Grüne Gentechnik - was ist das? "Grüne Gentechnik" ist laut Gentechnik-Wörterbuch eine "umgangssprachliche Bezeichnung für gentechnische Forschung mit Pflanzen, während
Molekulare Klonierung Praktikum
 Molekulare Klonierung Praktikum 2013 Praktikumsaufgabe Ligation 1. Zusammensetzung des Ligationsreaktions-ansatzes : 1 l Vektor DNA 1 l Insert DNA 2 l 10X Ligase Puffer 15 l destillertes Wasser 1 l Ligase
Molekulare Klonierung Praktikum 2013 Praktikumsaufgabe Ligation 1. Zusammensetzung des Ligationsreaktions-ansatzes : 1 l Vektor DNA 1 l Insert DNA 2 l 10X Ligase Puffer 15 l destillertes Wasser 1 l Ligase
Zellbiologie und Physiologie Labormethoden der Biologie
 Zellbiologie und Physiologie Labormethoden der Biologie Molekularbiologie I Dr. Stefan Weinl > Molekularbiologie I Plasmidpräparation Transformation Restriktionsverdau Gel-Elektrophorese 1 > Experimenteller
Zellbiologie und Physiologie Labormethoden der Biologie Molekularbiologie I Dr. Stefan Weinl > Molekularbiologie I Plasmidpräparation Transformation Restriktionsverdau Gel-Elektrophorese 1 > Experimenteller
Abbildungs- und Tabellenverzeichnis Abkürzungsverzeichnis Genbezeichnung. 1. Einleitung 1
 Abbildungs- und Tabellenverzeichnis Abkürzungsverzeichnis Genbezeichnung VI VIII X 1. Einleitung 1 1.1 Das Plastom 1 1.2 Transkription in Chloroplasten 4 1.2.1 Die plastidäre Transkriptionsmaschinerie
Abbildungs- und Tabellenverzeichnis Abkürzungsverzeichnis Genbezeichnung VI VIII X 1. Einleitung 1 1.1 Das Plastom 1 1.2 Transkription in Chloroplasten 4 1.2.1 Die plastidäre Transkriptionsmaschinerie
Transgene Organismen
 Transgene Organismen Themenübersicht 1) Einführung 2) Komplementäre DNA (cdna) 3) Vektoren 4) Einschleusung von Genen in Eukaryontenzellen 5) Ausmaß der Genexpression 6) Genausschaltung (Gen-Knockout)
Transgene Organismen Themenübersicht 1) Einführung 2) Komplementäre DNA (cdna) 3) Vektoren 4) Einschleusung von Genen in Eukaryontenzellen 5) Ausmaß der Genexpression 6) Genausschaltung (Gen-Knockout)
Inhaltsverzeichnis. 1 Was bitte ist denn»molekularbiologie«? Einige grundlegende Methoden... 13
 Inhaltsverzeichnis 1 Was bitte ist denn»molekularbiologie«?............... 1 1.1 Das Substrat der Molekularbiologie, oder: Molli-World für Anfänger...... 2 1.2 Was brauche ich zum Arbeiten?....................
Inhaltsverzeichnis 1 Was bitte ist denn»molekularbiologie«?............... 1 1.1 Das Substrat der Molekularbiologie, oder: Molli-World für Anfänger...... 2 1.2 Was brauche ich zum Arbeiten?....................
Ein interessanter und arbeitsreicher Tag im livfe Biolab in Darmstadt
 Ein interessanter und arbeitsreicher Tag im livfe Biolab in Darmstadt Als einer der ersten Kurse überhaupt durfte der Biologieleistungskurs der Alfred-Delp-Schule unter Kursleitung von Sven Remdisch das
Ein interessanter und arbeitsreicher Tag im livfe Biolab in Darmstadt Als einer der ersten Kurse überhaupt durfte der Biologieleistungskurs der Alfred-Delp-Schule unter Kursleitung von Sven Remdisch das
1. Grundoperationen der Gentechnik Schneiden von DNA
 1. Grundoperationen der Gentechnik Schneiden von DNA Eines der wichtigsten Werkzeuge der Gentechnik sind Restriktionsenzyme. Sie dienen sowohl dazu, die DNA aus dem Spenderorganismus in Bruchstücke zu
1. Grundoperationen der Gentechnik Schneiden von DNA Eines der wichtigsten Werkzeuge der Gentechnik sind Restriktionsenzyme. Sie dienen sowohl dazu, die DNA aus dem Spenderorganismus in Bruchstücke zu
Stammzüchtung. Selektion von natürlichen Varianten. Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese
 Stammzüchtung Selektion von natürlichen Varianten Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese Kreuzungen genetische Rekombination Sexuelle Kreuzungen Induzierte Zellfusion
Stammzüchtung Selektion von natürlichen Varianten Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese Kreuzungen genetische Rekombination Sexuelle Kreuzungen Induzierte Zellfusion
Methodensammlung des LAG PCR-Nachweis von gentechnisch veränderten Organismen, die von pbr322 abgeleitete Sequenzen enthalten
 Methodensammlung des LAG PCR-Nachweis von gentechnisch veränderten Organismen, die von pbr322 abgeleitete Sequenzen enthalten erstellt vom Unterausschuß Methodenentwicklung des LAG 1. Zweck und Anwendungsbereich
Methodensammlung des LAG PCR-Nachweis von gentechnisch veränderten Organismen, die von pbr322 abgeleitete Sequenzen enthalten erstellt vom Unterausschuß Methodenentwicklung des LAG 1. Zweck und Anwendungsbereich
Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers
 Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers Protein Expression Genomische DNA PCR Vektormolekül (Plasmid) Escherichia coli Reinigung Protein Transformation des Expressionsstammes
Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers Protein Expression Genomische DNA PCR Vektormolekül (Plasmid) Escherichia coli Reinigung Protein Transformation des Expressionsstammes
1. Beschreiben Sie die Rolle der folgenden Proteine bei der DNA- Replikation in E. coli:
 1. Beschreiben Sie die Rolle der folgenden Proteine bei der DNA- Replikation in E. coli: Übung 7 - DnaA bindet an 13 bp DNA Sequenz (DnaA Box, 5 Wiederholungen bei E. coli) im oric ori wird in AT reicher
1. Beschreiben Sie die Rolle der folgenden Proteine bei der DNA- Replikation in E. coli: Übung 7 - DnaA bindet an 13 bp DNA Sequenz (DnaA Box, 5 Wiederholungen bei E. coli) im oric ori wird in AT reicher
Thema Gentechnologie. Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #
 Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #2 06. 05. 2014 Restriktionsenzyme (http://rebase.neb.com) Statistik:Enzymes: Total: 15093 Restriction Enzymes 3945 Type I
Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #2 06. 05. 2014 Restriktionsenzyme (http://rebase.neb.com) Statistik:Enzymes: Total: 15093 Restriction Enzymes 3945 Type I
Inhaltsverzeichnis. Polymerase Chain Reaction Theoretischer Hintergrund - 2 -
 Inhaltsverzeichnis 1 Theoretischer Hintergrund - 2-1.1 Die Komponenten der PCR - 2-1.2 Das Verfahren der PCR - 3-1.3 Die Gelelektrophorese - 5-2 Material und Methoden - 6-3 Ergebnisse - 7-3.1 Ergebnisse
Inhaltsverzeichnis 1 Theoretischer Hintergrund - 2-1.1 Die Komponenten der PCR - 2-1.2 Das Verfahren der PCR - 3-1.3 Die Gelelektrophorese - 5-2 Material und Methoden - 6-3 Ergebnisse - 7-3.1 Ergebnisse
MPP Multiplex 2x PCR-Mastermix
 Datenblatt Artikel-Nr. BS91.522.0250 250 Reaktionen in 20µl Artikel-Nr. BS91.522.1250 1250 Reaktionen a 20µl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
Datenblatt Artikel-Nr. BS91.522.0250 250 Reaktionen in 20µl Artikel-Nr. BS91.522.1250 1250 Reaktionen a 20µl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
Zellbiologie und Physiologie Labormethoden der Biologie
 Zellbiologie und Physiologie Labormethoden der Biologie > Molekularbiologie I Plasmidpräparation Molekularbiologie I Transformation Gel-Elektrophorese Dr. Stefan Weinl > Plasmid-Isolierung aus E. coli
Zellbiologie und Physiologie Labormethoden der Biologie > Molekularbiologie I Plasmidpräparation Molekularbiologie I Transformation Gel-Elektrophorese Dr. Stefan Weinl > Plasmid-Isolierung aus E. coli
Musterlösung- Übung 9
 Teil Molekularbiologie 1. Über Mutationen a) In welchem Teil eines Operons befinden sich Mutationen, welche die Menge eines Enzyms in einem Organismus beeinflussen? Solche Mutationen befinden sich im Operator.
Teil Molekularbiologie 1. Über Mutationen a) In welchem Teil eines Operons befinden sich Mutationen, welche die Menge eines Enzyms in einem Organismus beeinflussen? Solche Mutationen befinden sich im Operator.
Materialien und Methoden...16
 Inhaltsverzeichnis I. Einleitung...1 1. Mitochondrien - Energielieferanten der eukaryontischen Zelle... 1 2. Die mitochondriale DNA-Replikation... 5 2.1. Transkriptionsabhängige mtdna-replikation... 5
Inhaltsverzeichnis I. Einleitung...1 1. Mitochondrien - Energielieferanten der eukaryontischen Zelle... 1 2. Die mitochondriale DNA-Replikation... 5 2.1. Transkriptionsabhängige mtdna-replikation... 5
Produktkatalog 2010. Molekularbiologische Reagenzien
 Produktion, Vertrieb und Serviceleistung im Bereich der Molekularbiologie und Medizin Produktkatalog 2010 Molekularbiologische Reagenzien Molegene GmbH Bienenweg 28 35764 Sinn Tel. 02772-570952 Fax 02772-570945
Produktion, Vertrieb und Serviceleistung im Bereich der Molekularbiologie und Medizin Produktkatalog 2010 Molekularbiologische Reagenzien Molegene GmbH Bienenweg 28 35764 Sinn Tel. 02772-570952 Fax 02772-570945
S-Dis Hotstart Polymerase
 Datenblatt Artikel-Nr. BS91.219.0200 Artikel-Nr. BS91.219.1000 200 Units 1000 Units (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen: Farbe: 1 Beschreibung Die
Datenblatt Artikel-Nr. BS91.219.0200 Artikel-Nr. BS91.219.1000 200 Units 1000 Units (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen: Farbe: 1 Beschreibung Die
Methoden der Gentechnik
 Methoden der Gentechnik *** DNA-Rekombination und Klonierung *** 1. Allgemeine Grundprinzipien 1.1. Wesen der Gentechnik 1.2. Allgemeine Ziele der Gentechnik 1.3. Molekulare Voraussetzungen 1.4. Wichtige
Methoden der Gentechnik *** DNA-Rekombination und Klonierung *** 1. Allgemeine Grundprinzipien 1.1. Wesen der Gentechnik 1.2. Allgemeine Ziele der Gentechnik 1.3. Molekulare Voraussetzungen 1.4. Wichtige
5x QPCR Mix (ROX) Datenblatt. Artikel-Nr. BS µl Artikel-Nr. BS µl. (Nur für Forschung und in vitro-anwendungen)
 Datenblatt Artikel-Nr. BS76.520.0200 200 µl Artikel-Nr. BS76.520.1000 1.000 µl Artikel-Nr. BS76.520.5000 5.000 µl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
Datenblatt Artikel-Nr. BS76.520.0200 200 µl Artikel-Nr. BS76.520.1000 1.000 µl Artikel-Nr. BS76.520.5000 5.000 µl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
DNA-KLONIERUNG.
 DNA-KLONIERUNG http://openpcr.org/use-it/ DNA- KLONIERUNG: Vervielvältigung eines DNA-Moleküls In vitro - PCR In vivo in unterschiedlichen Wirtszellen POLYMERASE- KETTENREAKTION (Polymerase Chain Reaction,
DNA-KLONIERUNG http://openpcr.org/use-it/ DNA- KLONIERUNG: Vervielvältigung eines DNA-Moleküls In vitro - PCR In vivo in unterschiedlichen Wirtszellen POLYMERASE- KETTENREAKTION (Polymerase Chain Reaction,
Aufbau eines Assays zur Optimierung einer Polymerase für die Generierung hochgradig fluoreszenz-markierter DNA
 Aufbau eines Assays zur Optimierung einer Polymerase für die Generierung hochgradig fluoreszenz-markierter DNA Von der Naturwissenschaftlichen Fakultät der Technischen Universität Carolo-Wilhelmina zu
Aufbau eines Assays zur Optimierung einer Polymerase für die Generierung hochgradig fluoreszenz-markierter DNA Von der Naturwissenschaftlichen Fakultät der Technischen Universität Carolo-Wilhelmina zu
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
Rekombinante DNA. Werkzeuge der Gentechnik
 Rekombinante DNA = im Labor neu zusammengesetzte DNA. Ein definiertes DNA Fragment (meistens ein Gen) wird aus seiner ursprünglichen Lage entnommen und in einen Vektor integriert, der gezielt in andere
Rekombinante DNA = im Labor neu zusammengesetzte DNA. Ein definiertes DNA Fragment (meistens ein Gen) wird aus seiner ursprünglichen Lage entnommen und in einen Vektor integriert, der gezielt in andere
Mikrobiologie Praktikum SS 2001 Montag, den Sarah Horsten Gruppe 3. Hinweise
 Montag, den 01.10.2002 Sarah Horsten Gruppe 3 Hinweise Dies sind Protokolle zum Praktikum Genetik und Molekularbiologie an dem ich im SS 2001 teilgenommen habe. Natürlich haben meine Protokolle keinen
Montag, den 01.10.2002 Sarah Horsten Gruppe 3 Hinweise Dies sind Protokolle zum Praktikum Genetik und Molekularbiologie an dem ich im SS 2001 teilgenommen habe. Natürlich haben meine Protokolle keinen
Grundlagen der Klonierung. Analytische Methoden der Biologie SS09 7 Klonierung und Gentechnik. Modul
 Restriktion und Ligation: Restriktion und Ligation: Grundlagen der Klonierung Modul 2303-021 1 Restriktion und Ligation Verknüpfung von Fragmenten unterschiedlicher DNA Herkunft Restriktion und Ligation
Restriktion und Ligation: Restriktion und Ligation: Grundlagen der Klonierung Modul 2303-021 1 Restriktion und Ligation Verknüpfung von Fragmenten unterschiedlicher DNA Herkunft Restriktion und Ligation
Molekularbiologische / gentechnische Methoden
 Molekularbiologische / gentechnische Methoden MPM 1 Wie lässt sich ein spezifisches Gen/Genprodukt molekular analysieren? Fundamentales Problem: Komplexität biologischer Systeme MPM 2 Ein Ausschnitt aus
Molekularbiologische / gentechnische Methoden MPM 1 Wie lässt sich ein spezifisches Gen/Genprodukt molekular analysieren? Fundamentales Problem: Komplexität biologischer Systeme MPM 2 Ein Ausschnitt aus
Grundideen der Gentechnik
 Grundideen der Gentechnik Die Gentechnik kombiniert Biotechnik und Züchtung. Wie in der Züchtung wird die Erbinformation eines Lebewesen verändert. Dabei nutzte man in den Anfängen der Gentechnik vor allem
Grundideen der Gentechnik Die Gentechnik kombiniert Biotechnik und Züchtung. Wie in der Züchtung wird die Erbinformation eines Lebewesen verändert. Dabei nutzte man in den Anfängen der Gentechnik vor allem
Vertiefendes Seminar zur Vorlesung Biochemie I
 Vertiefendes Seminar zur Vorlesung Biochemie I 30.01.2015 Klausurvorbereitung: Gerhild van Echten-Deckert Rekombinante DNA Fon. +49-228-732703 Homepage: http://www.limes.uni-bonn.de Klärung einiger Begriffe:
Vertiefendes Seminar zur Vorlesung Biochemie I 30.01.2015 Klausurvorbereitung: Gerhild van Echten-Deckert Rekombinante DNA Fon. +49-228-732703 Homepage: http://www.limes.uni-bonn.de Klärung einiger Begriffe:
» PCR « Taq Polymerase S. Taq Polymerase E. Pwo Polymerase. Pfu Polymerase. ReproHot Proofreading Polymerase. ReproFast Proofreading Polymerase
 Standard PCR Taq Polymerase S Taq DNA Polymerase S für hohe Selektivität von 100 bp bis 10 kb ist eine hochprozessive 5'- 3' DNA Polymerase ohne 3'- 5' Exonukleaseaktivität. M3001.0250 250 units 50,00
Standard PCR Taq Polymerase S Taq DNA Polymerase S für hohe Selektivität von 100 bp bis 10 kb ist eine hochprozessive 5'- 3' DNA Polymerase ohne 3'- 5' Exonukleaseaktivität. M3001.0250 250 units 50,00
Aufgabe 1. Bakterien als Untersuchungsgegenstand!
 Genetik I Aufgabe 1. Bakterien als Untersuchungsgegenstand 1. Beschriften Sie die Abbildung zu den Bakterien. 2. Nennen Sie Vorteile, die Bakterien wie Escherichia coli so wertvoll für die genetische Forschung
Genetik I Aufgabe 1. Bakterien als Untersuchungsgegenstand 1. Beschriften Sie die Abbildung zu den Bakterien. 2. Nennen Sie Vorteile, die Bakterien wie Escherichia coli so wertvoll für die genetische Forschung
F-I Molekulare Zoologie: Teil I: Expressionsanalysen. Expressionsanalyse mittels RT-PCR
 F-I Molekulare Zoologie: Teil I: Expressionsanalysen Expressionsanalyse mittels RT-PCR Inhalt: Seite I. Generelles 1 II. RNA-Aufreinigung mit EZNA Total RNA Kit (PeqLab)...2 III. Umschreiben von RNA in
F-I Molekulare Zoologie: Teil I: Expressionsanalysen Expressionsanalyse mittels RT-PCR Inhalt: Seite I. Generelles 1 II. RNA-Aufreinigung mit EZNA Total RNA Kit (PeqLab)...2 III. Umschreiben von RNA in
Stammzüchtung. Selektion von natürlichen Varianten. Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese
 Stammzüchtung Selektion von natürlichen Varianten Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese Kreuzungen genetische Rekombination Sexuelle Kreuzungen Induzierte Zellfusion
Stammzüchtung Selektion von natürlichen Varianten Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese Kreuzungen genetische Rekombination Sexuelle Kreuzungen Induzierte Zellfusion
3.5 Moderne Genetik - Vorgänge
 3.5 Moderne Genetik - Vorgänge Der genetische Code Jedes Gen besteht aus sogenannten Basentriplets. Das ist eine Sequenz von drei aufeinanderfolgenden Nukleinbasen, die für eine bestimmte Aminosäure stehen.
3.5 Moderne Genetik - Vorgänge Der genetische Code Jedes Gen besteht aus sogenannten Basentriplets. Das ist eine Sequenz von drei aufeinanderfolgenden Nukleinbasen, die für eine bestimmte Aminosäure stehen.
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
1 Einleitung Geschichte der DNase I DNase I: Proteinstruktur und Isoformen DNase I: Biochemische Eigenschaften 6
 Inhaltsverzeichnis 1 Einleitung 1 1.1 Geschichte der DNase I 2 1.2 DNase I: Proteinstruktur und Isoformen 4 1.3 DNase I: Biochemische Eigenschaften 6 1.4 DNase I-Genfamilie 8 1.4.1 DNase γ (DNase Y/ DNAS1L3/
Inhaltsverzeichnis 1 Einleitung 1 1.1 Geschichte der DNase I 2 1.2 DNase I: Proteinstruktur und Isoformen 4 1.3 DNase I: Biochemische Eigenschaften 6 1.4 DNase I-Genfamilie 8 1.4.1 DNase γ (DNase Y/ DNAS1L3/
Vererbung. Die durch Fortpflanzung entstandene Nachkommenschaft gleicht den Elternorganismen weitgehend
 Vererbung Die durch Fortpflanzung entstandene Nachkommenschaft gleicht den Elternorganismen weitgehend Klassische Genetik Äußeres Erscheinungsbild: Phänotypus setzt sich aus einer Reihe von Merkmalen (Phänen))
Vererbung Die durch Fortpflanzung entstandene Nachkommenschaft gleicht den Elternorganismen weitgehend Klassische Genetik Äußeres Erscheinungsbild: Phänotypus setzt sich aus einer Reihe von Merkmalen (Phänen))
Gentechnologie: Klonierung und Transformation von DNA
 Grundpraktikum Genetik 8. Kurstag 16.06.2005 Gentechnologie: Klonierung und Transformation von DNA Lerninhalte: Transformation, natürliche Kompetenz, Transformationseffizienz, Vektor, Plasmid, Resistenzgen,
Grundpraktikum Genetik 8. Kurstag 16.06.2005 Gentechnologie: Klonierung und Transformation von DNA Lerninhalte: Transformation, natürliche Kompetenz, Transformationseffizienz, Vektor, Plasmid, Resistenzgen,
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 3. Aus welchen vier Nukleotiden ist RNA aufgebaut? 4. DNA RNA 5. Ein Wissenschaftler
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 3. Aus welchen vier Nukleotiden ist RNA aufgebaut? 4. DNA RNA 5. Ein Wissenschaftler
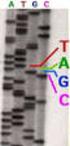
1. Nennt Informationen, die ein Wissenschaftler für die Durchführung des farbig markierten Schrittes benötigt. 2. Nennt zusätzliche Probleme die bei
 Wir erinnern uns 1. Nennt Informationen, die ein Wissenschaftler für die Durchführung des farbig markierten Schrittes benötigt. 2. Nennt zusätzliche Probleme die bei der Verwendung eines Gens aus einer
Wir erinnern uns 1. Nennt Informationen, die ein Wissenschaftler für die Durchführung des farbig markierten Schrittes benötigt. 2. Nennt zusätzliche Probleme die bei der Verwendung eines Gens aus einer
Jens Tilsner (Autor) Aminosäuretransport in Raps unter besonderer Berücksichtigung des Entwicklungsstadiums der Pflanze und der Stickstoffdüngung
 Jens Tilsner (Autor) Aminosäuretransport in Raps unter besonderer Berücksichtigung des Entwicklungsstadiums der Pflanze und der Stickstoffdüngung https://cuvillier.de/de/shop/publications/3133 Copyright:
Jens Tilsner (Autor) Aminosäuretransport in Raps unter besonderer Berücksichtigung des Entwicklungsstadiums der Pflanze und der Stickstoffdüngung https://cuvillier.de/de/shop/publications/3133 Copyright:
Klonierung von S2P Rolle der M19-Zellen. POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel
 Klonierung von S2P Rolle der M19-Zellen POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel Inhalt 1. Was ist eine humane genomische DNA-Bank? 2. Unterschied zwischen cdna-bank und genomischer DNA-Bank?
Klonierung von S2P Rolle der M19-Zellen POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel Inhalt 1. Was ist eine humane genomische DNA-Bank? 2. Unterschied zwischen cdna-bank und genomischer DNA-Bank?
Abbildungsverzeichnis. Tabellenverzeichnis. Abkürzungsverzeichnis. 1 Einleitung 1
 Inhaltsverzeichnis Inhaltsverzeichnis I Abbildungsverzeichnis VI Tabellenverzeichnis VIII Abkürzungsverzeichnis IX 1 Einleitung 1 1.1 Wasser, ein limitierender Faktor für die Landwirtschaft 1 1.2 Anpassungen
Inhaltsverzeichnis Inhaltsverzeichnis I Abbildungsverzeichnis VI Tabellenverzeichnis VIII Abkürzungsverzeichnis IX 1 Einleitung 1 1.1 Wasser, ein limitierender Faktor für die Landwirtschaft 1 1.2 Anpassungen
Gentechnologie fur Einsteiger
 T. A. Brown Gentechnologie fur Einsteiger 6. Auflage ubersetzt von Sebastian Grundprinzipien der Klonierung und 1 1 Klonierung und DNA-Analyse so wichtig? 3 Friihe Entwicklungen in der Genetik 4 1.2 Die
T. A. Brown Gentechnologie fur Einsteiger 6. Auflage ubersetzt von Sebastian Grundprinzipien der Klonierung und 1 1 Klonierung und DNA-Analyse so wichtig? 3 Friihe Entwicklungen in der Genetik 4 1.2 Die
DNA Isolierung. Praktikum Dr. László Kredics
 Isolierung Praktikum Dr. László Kredics SZTE, Inst. für Med. Biol., Praktikum -Isolierung Zellaufschluss Isolierung genomischer Isolierung von Plasmid Konzentrationsbestimmung der -Lösungen Anhand Absorptionswert
Isolierung Praktikum Dr. László Kredics SZTE, Inst. für Med. Biol., Praktikum -Isolierung Zellaufschluss Isolierung genomischer Isolierung von Plasmid Konzentrationsbestimmung der -Lösungen Anhand Absorptionswert
5x QPCR Mix EvaGreen (ROX)
 Datenblatt Artikel-Nr. BS76.580.0200 200 µl Artikel-Nr. BS76.580.1000 1.000 µl Artikel-Nr. BS76.580.5000 5.000 µl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
Datenblatt Artikel-Nr. BS76.580.0200 200 µl Artikel-Nr. BS76.580.1000 1.000 µl Artikel-Nr. BS76.580.5000 5.000 µl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
Gentechnologie für Einsteiger
 T. A. Brown Gentechnologie für Einsteiger 3. Auflage Aus dem Englischen übersetzt von Sebastian Vogel Spektrum Akademischer Verlag Heidelberg Berlin Vorwort Vorwort zur dritten englischen Auflage Vorwort
T. A. Brown Gentechnologie für Einsteiger 3. Auflage Aus dem Englischen übersetzt von Sebastian Vogel Spektrum Akademischer Verlag Heidelberg Berlin Vorwort Vorwort zur dritten englischen Auflage Vorwort
vwf-agarose Datenblatt (Nur für die Forschung) Artikel-Nr. BS Mindestens haltbar bis: Bio&SELL
 Datenblatt Artikel-Nr. BS 20.50.005 Artikel-Nr. BS 20.50.100 5g 100g (Nur für die Forschung) Chargen-Nr.: BS819661.5 Mindestens haltbar bis: 07-2020 Aussehen: homogenes Pulver Farbe: weiß 1 Beschreibung
Datenblatt Artikel-Nr. BS 20.50.005 Artikel-Nr. BS 20.50.100 5g 100g (Nur für die Forschung) Chargen-Nr.: BS819661.5 Mindestens haltbar bis: 07-2020 Aussehen: homogenes Pulver Farbe: weiß 1 Beschreibung
Molekularbiologie 2 - Wer war am Tatort?
 Molekularbiologie 2 - Wer war am Tatort? DNA-Tatortanalyse Genetischer Fingerabdruck Inhaltsverzeichnis Theoretischer Teil... 2 1. Der genetische Fingerabdruck Ausgangslage der Analyse... 2 2. Die Polymerase-Ketten-Reaktion
Molekularbiologie 2 - Wer war am Tatort? DNA-Tatortanalyse Genetischer Fingerabdruck Inhaltsverzeichnis Theoretischer Teil... 2 1. Der genetische Fingerabdruck Ausgangslage der Analyse... 2 2. Die Polymerase-Ketten-Reaktion
2.1 Das prä-mrna Spleißen 3
 I 1. Zusammenfassung 1 2. Einleitung 3 2.1 Das prä-mrna Spleißen 3 2.1.1 Die Konsensussequenzen zweier Klassen von prä-mrna Introns 3 2.1.2 Die katalytischen Transesterifizierungsreaktionen 5 2.2 Das U2-abhängige
I 1. Zusammenfassung 1 2. Einleitung 3 2.1 Das prä-mrna Spleißen 3 2.1.1 Die Konsensussequenzen zweier Klassen von prä-mrna Introns 3 2.1.2 Die katalytischen Transesterifizierungsreaktionen 5 2.2 Das U2-abhängige
High Yield-Polymerase
 Datenblatt Artikel-Nr. BS91.221.0200 Artikel-Nr. BS91.221.1000 200 Units 1000 Units (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen: Farbe: 1 Beschreibung Der
Datenblatt Artikel-Nr. BS91.221.0200 Artikel-Nr. BS91.221.1000 200 Units 1000 Units (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen: Farbe: 1 Beschreibung Der
Zentrales Dogma der Biologie
 Zentrales Dogma der Biologie Transkription: von der DNA zur RNA Biochemie 01/1 Transkription Biochemie 01/2 Transkription DNA: RNA: Biochemie 01/3 Transkription DNA: RNA: Biochemie 01/4 Transkription RNA:
Zentrales Dogma der Biologie Transkription: von der DNA zur RNA Biochemie 01/1 Transkription Biochemie 01/2 Transkription DNA: RNA: Biochemie 01/3 Transkription DNA: RNA: Biochemie 01/4 Transkription RNA:
Es ist die Zeit gekommen, zu verstehen, wie es zur Proteinbiosynthese kommt?! Wobei jeweils eine AS von 3 Basen codiert wird..
 Proteinbiosynthese Es ist die Zeit gekommen, zu verstehen, wie es zur Proteinbiosynthese kommt?! Alle Proteine, sind über die DNA codiert Wobei jeweils eine AS von 3 Basen codiert wird.. GENETISCHER CODE
Proteinbiosynthese Es ist die Zeit gekommen, zu verstehen, wie es zur Proteinbiosynthese kommt?! Alle Proteine, sind über die DNA codiert Wobei jeweils eine AS von 3 Basen codiert wird.. GENETISCHER CODE
Es gibt derzeit über 300 kommerziell erhältliche Restriktionsenzyme, die die DNA entweder glatt (blunt) oder überhängend (sticky) spalten.
 4.3 Gentechnologie Bakteriophagen sind Viren, die prokaryontische Zellen befallen. Hierzu dockt der Phage an der bakteriellen Zellmembran an und injiziert sein Genom in das Cytoplasma. Das virale Genom
4.3 Gentechnologie Bakteriophagen sind Viren, die prokaryontische Zellen befallen. Hierzu dockt der Phage an der bakteriellen Zellmembran an und injiziert sein Genom in das Cytoplasma. Das virale Genom
C. R. Newton A. Graham 12'CR. 2. Auflage
 C. R. Newton A. Graham 12'CR 2. Auflage Vorwort 1 1 Danksagung 13 Abkürzungen 1 4 Teil 1 : Die wesentlichen Prinzipien und Methoden 1. Die Polymerasekettenreaktion (PCR) 19 1.1 Literatur 26 2. Geräte,
C. R. Newton A. Graham 12'CR 2. Auflage Vorwort 1 1 Danksagung 13 Abkürzungen 1 4 Teil 1 : Die wesentlichen Prinzipien und Methoden 1. Die Polymerasekettenreaktion (PCR) 19 1.1 Literatur 26 2. Geräte,
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 7 (11.07-15.07.) Methoden und Techniken II 1. Sie bekommen
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 7 (11.07-15.07.) Methoden und Techniken II 1. Sie bekommen
Novartis Pharma AG Schullabor. Plasmid-DNA. Auf der Suche nach dem Antibiotikaresistenz Gen 2019 / 1
 Novartis Pharma AG Schullabor Plasmid-DNA Auf der Suche nach dem Antibiotikaresistenz Gen 019 / 1 Herausgeber Novartis Pharma AG, CH-00 Basel Kontaktadresse: Novartis Pharma AG Schullabor WKL-1..6A Postfach
Novartis Pharma AG Schullabor Plasmid-DNA Auf der Suche nach dem Antibiotikaresistenz Gen 019 / 1 Herausgeber Novartis Pharma AG, CH-00 Basel Kontaktadresse: Novartis Pharma AG Schullabor WKL-1..6A Postfach
Methoden Sebők Ágnes
 Methoden 1. 09.11.2004 Sebők Ágnes 1 2 Molekulare Zellbiologie Molekularbiologische Methode I. DNA 3 DNA-Struktur Primärstruktur: Sequenz der Nucleotiden, lineare Polymer, Phosphodiestherbindungen Sekundärstruktur:
Methoden 1. 09.11.2004 Sebők Ágnes 1 2 Molekulare Zellbiologie Molekularbiologische Methode I. DNA 3 DNA-Struktur Primärstruktur: Sequenz der Nucleotiden, lineare Polymer, Phosphodiestherbindungen Sekundärstruktur:
Robin Martin. Elektrophorese. von Nucleinsäuren
 Robin Martin Elektrophorese von Nucleinsäuren Abkürzungen 11 Vorwort 13 Danksagung 15 I. Grundprinzipien und Methoden 1. Einleitung: Verschiedene Arten und Formen von Nucleinsäure 19 1.1 Überblick 19
Robin Martin Elektrophorese von Nucleinsäuren Abkürzungen 11 Vorwort 13 Danksagung 15 I. Grundprinzipien und Methoden 1. Einleitung: Verschiedene Arten und Formen von Nucleinsäure 19 1.1 Überblick 19
2.1 Die Entstehung des Gehirns aus neuralen Stammzellen Transkriptionsfaktoren in der Gehirnentwicklung...16
 Inhaltsverzeichnis Danksagung...3 Inhaltsverzeichnis...5 Abkürzungverzeichnis...1 1 Zielsetzung...4 2 Einleitung...6 2.1 Die Entstehung des Gehirns aus neuralen Stammzellen...6 2.2 Radiale Gliazellen...9
Inhaltsverzeichnis Danksagung...3 Inhaltsverzeichnis...5 Abkürzungverzeichnis...1 1 Zielsetzung...4 2 Einleitung...6 2.1 Die Entstehung des Gehirns aus neuralen Stammzellen...6 2.2 Radiale Gliazellen...9
DNA-Replikation. Konrad Beyreuther. Stefan Kins
 DNA-Replikation Konrad Beyreuther Stefan Kins DNA-Replikation Originalgetreue Verdopplung des genetischen Materials als Voraussetzung für die kontinuierliche Weitergabe der in der DNA verschlüsselten Information
DNA-Replikation Konrad Beyreuther Stefan Kins DNA-Replikation Originalgetreue Verdopplung des genetischen Materials als Voraussetzung für die kontinuierliche Weitergabe der in der DNA verschlüsselten Information
DNA Replikation ist semikonservativ. Abb. aus Stryer (5th Ed.)
 DNA Replikation ist semikonservativ Entwindung der DNA-Doppelhelix durch eine Helikase Replikationsgabel Eltern-DNA Beide DNA-Stränge werden in 5 3 Richtung synthetisiert DNA-Polymerasen katalysieren die
DNA Replikation ist semikonservativ Entwindung der DNA-Doppelhelix durch eine Helikase Replikationsgabel Eltern-DNA Beide DNA-Stränge werden in 5 3 Richtung synthetisiert DNA-Polymerasen katalysieren die
Biochemie Vorlesung Die ersten 100 Seiten
 Biochemie Vorlesung 11-15 Die ersten 100 Seiten 1. Unterschiede der Zellen Eukaryoten- Prokaryoten Eukaryoten: - Keine Zellwand - Intrazelluläre Membransysteme - Kernhülle mit 2 Membranen und Kernporen
Biochemie Vorlesung 11-15 Die ersten 100 Seiten 1. Unterschiede der Zellen Eukaryoten- Prokaryoten Eukaryoten: - Keine Zellwand - Intrazelluläre Membransysteme - Kernhülle mit 2 Membranen und Kernporen
Die gewebespezifische Genexpression in der Epidermis des Gerstenblattes
 Die gewebespezifische Genexpression in der Epidermis des Gerstenblattes Dissertation zur Erlangung des naturwissenschaftlichen Doktorgrades der Bayerischen Julius-Maximilians-Universität Würzburg vorgelegt
Die gewebespezifische Genexpression in der Epidermis des Gerstenblattes Dissertation zur Erlangung des naturwissenschaftlichen Doktorgrades der Bayerischen Julius-Maximilians-Universität Würzburg vorgelegt
Pflanze direkt 2x PCR-Mastermix
 Datenblatt Artikel-Nr. BS91.322.0250 Artikel-Nr. BS91.322.1250 250 Reaktionen in 20 μl 1250 Reaktionen in 20 μl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
Datenblatt Artikel-Nr. BS91.322.0250 Artikel-Nr. BS91.322.1250 250 Reaktionen in 20 μl 1250 Reaktionen in 20 μl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Vorbemerkung für die Erlangung des Testats: Bearbeiten Sie die unten gestellten Aufgaben
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Vorbemerkung für die Erlangung des Testats: Bearbeiten Sie die unten gestellten Aufgaben
Gentechnik - Klonieren und Analysieren von Genen
 Gentechnik - Klonieren und Analysieren von Genen In den letzten Jahren wurden zahlreiche Methoden entwickelt, die es erlauben, das genetische Material nahezu beliebig zu verändern und gezielt neu zu kombinieren,
Gentechnik - Klonieren und Analysieren von Genen In den letzten Jahren wurden zahlreiche Methoden entwickelt, die es erlauben, das genetische Material nahezu beliebig zu verändern und gezielt neu zu kombinieren,
Gentechnik - Klonieren und Analysieren von Genen
 Gentechnik - Klonieren und Analysieren von Genen In den letzten Jahren wurden zahlreiche Methoden entwickelt, die es erlauben, das genetische Material nahezu beliebig zu verändern und gezielt neu zu kombinieren,
Gentechnik - Klonieren und Analysieren von Genen In den letzten Jahren wurden zahlreiche Methoden entwickelt, die es erlauben, das genetische Material nahezu beliebig zu verändern und gezielt neu zu kombinieren,
https://cuvillier.de/de/shop/publications/2978
 Andreas Christmann (Autor) Zur bakteriellen Oberflächenpräsentation kombinatorischer Peptidbibliotheken und deren Anwendung auf Fragestellungen der Immunologie, Molekularbiologie und der Molekualren Medizin
Andreas Christmann (Autor) Zur bakteriellen Oberflächenpräsentation kombinatorischer Peptidbibliotheken und deren Anwendung auf Fragestellungen der Immunologie, Molekularbiologie und der Molekualren Medizin
Einführung in die Umweltwissenschaften
 Einführung in die Umweltwissenschaften Genetik und Gentechnologie (pro und contra) 16.11. 2012 WS 2011/12 H.P. Aubauer, P. Bajons, V. Schlosser Basen:? Purinbasen: Adenin DNA - Grundbausteine Guanin Phosphate
Einführung in die Umweltwissenschaften Genetik und Gentechnologie (pro und contra) 16.11. 2012 WS 2011/12 H.P. Aubauer, P. Bajons, V. Schlosser Basen:? Purinbasen: Adenin DNA - Grundbausteine Guanin Phosphate
Inhalt Genexpression Microarrays E-Northern
 Inhalt Genexpression Microarrays E-Northern Genexpression Übersicht Definition Proteinbiosynthese Ablauf Transkription Translation Transport Expressionskontrolle Genexpression: Definition Realisierung
Inhalt Genexpression Microarrays E-Northern Genexpression Übersicht Definition Proteinbiosynthese Ablauf Transkription Translation Transport Expressionskontrolle Genexpression: Definition Realisierung
DNA enthält Gene. DNA Struktur. DNA Replikation. Gentransfer in Bakterien
 6. DNA Bakteriengenetik Konzepte: DNA enthält Gene DNA Struktur DNA Replikation Gentransfer in Bakterien Bakteriophagen 2. Welcher der folgenden Sätze entspricht der Chargaff Regel? A) Die Menge von Purinen
6. DNA Bakteriengenetik Konzepte: DNA enthält Gene DNA Struktur DNA Replikation Gentransfer in Bakterien Bakteriophagen 2. Welcher der folgenden Sätze entspricht der Chargaff Regel? A) Die Menge von Purinen
Fachverlag Köhler Giessen VETERINÄRMEDIZIN
 VETERINÄRMEDIZIN Kälteanpassung \bi\ Listeria monocytogenes: Klonierung, D^Ä-Sequenzanalyse und Funktionsstudien der Gene CS/JL, CS/JLB und flar aus dem Wildtypstamm Listeria monocytogenes EGD Eva-Maria
VETERINÄRMEDIZIN Kälteanpassung \bi\ Listeria monocytogenes: Klonierung, D^Ä-Sequenzanalyse und Funktionsstudien der Gene CS/JL, CS/JLB und flar aus dem Wildtypstamm Listeria monocytogenes EGD Eva-Maria
In den Proteinen der Lebewesen treten in der Regel 20 verschiedene Aminosäuren auf. Deren Reihenfolge muss in der Nucleotidsequenz der mrna und damit
 In den Proteinen der Lebewesen treten in der Regel 20 verschiedene Aminosäuren auf. Deren Reihenfolge muss in der Nucleotidsequenz der mrna und damit in der Nucleotidsequenz der DNA verschlüsselt (codiert)
In den Proteinen der Lebewesen treten in der Regel 20 verschiedene Aminosäuren auf. Deren Reihenfolge muss in der Nucleotidsequenz der mrna und damit in der Nucleotidsequenz der DNA verschlüsselt (codiert)
1. Welche Auswirkungen auf die Expression des lac-operons haben die folgenden Mutationen:
 Übung 10 1. Welche Auswirkungen auf die Expression des lac-operons haben die folgenden Mutationen: a. Eine Mutation, die zur Expression eines Repressors führt, der nicht mehr an den Operator binden kann.
Übung 10 1. Welche Auswirkungen auf die Expression des lac-operons haben die folgenden Mutationen: a. Eine Mutation, die zur Expression eines Repressors führt, der nicht mehr an den Operator binden kann.
