Vorlesung LV-Nr Molekularbiologie für Agrarwissenschaften. J. Glößl, SS 2007
|
|
|
- Ulrike Neumann
- vor 7 Jahren
- Abrufe
Transkript
1 Vorlesung LV-Nr Molekularbiologie für Agrarwissenschaften J. Glößl, SS 2007 Thematik: Molekularbiologische Methoden Teil 3 Die ppt Folien wurden freundlicherweise von Prof. Florian Rüker aus der Vorlesung Einführung in die Molekularbiologie, LV , bereitgestellt Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 1
2 Biotechnologisch relevante Expressionssysteme gemeint ist haupsächlich Herstellung von rekombinanten Proteinen Prokaryontisch: E. coli: rekombinante Proteine allgemein B. subtilis: hauptsächlich Proteasen (z.b. für Waschmittel: Subtilisin) Eukaryontisch: Hefe: Saccharomyces cerevisiae, Pichia pastoris Pilze: hauptsächlich Sekundärmetaboliten (Antibiotika,...) Säugerzellen: CHO (Chinese Hamster Ovary), Myelomzellen u.a. Insektenzellen transgene Tiere: z.b. Expression in der Milch mit ß-Casein Promoter transgene Pflanzen: Tabak, Mais u.a. Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 2
3 Expressionsvektoren Wie wird ein einfacher Klonierungsvektor zum Expressionsvektor? Elemente für Transkription Promoter, Terminator, Regulationssequenzen (z.b. lac Operator, lac Repressor, Introns) Elemente für Translation Ribosomenbindungsstelle (in Bakterien Shine-Dalgarno) Translation Initiationscodon (ATG, oder, selten GTG oder TTG) Translationterminationscodons (TAA, TGA, TAG) Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 3
4 Grundsätzliche Überlegungen zur Wahl des Expressionssystems Wofür soll das Produkt eingesetzt werden? Therapeutisch: höchste Anforderungen an Qualität Funktion Toxizität, Verträglichkeit Reinheit (Freiheit von Bestandteilen der Wirtszelle, des Mediums, von Abbauprodukten) Antigenizität Stabilität Authentizität (Struktur, posttranslationale Modifikationen) Reagens Funktion,... Anforderungen je nach Verwendung variabel Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 4
5 Grundsätzliche Überlegungen zur Wahl des Expressionssystems Quelle des zu exprimierenden Gens? Pro- bzw. eukaryontisch cdna oder genomisch synthetisch benötigte Proteinmenge? Ist natürlich ein entscheidender Faktor, das wichtigste ist aber immer die Qualität, d.h. was muß mein Protein können technische Möglichkeiten, Zeitbedarf Schüttelkolben, Fermentation, scale up Downstream processing, ev. Refolding von inclusion bodies Zeitrahmen: E. coli: Tage Hefe: Wochen tierische Zellen: Monate Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 5
6 Expressionsvektoren - Entscheidungen Selektion - dominant oder Komplementation einer Mutation? Induzierbare oder konstitutive Expression? Extrachromosomale Replikation oder Integration ins Genom? Intrazelluläre Expression oder Ausschleusung ins Medium? Soll ev. ein Fusionsprotein gemacht werden? Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 6
7 Transgene Tiere Übergeordnetes Prinzip ein kloniertes Gen wird in den Kern eines befruchteten Eies eingebracht Dieses Ei wird in ein scheinschwangeres (Behandlung mit Hormonen) Tier implantiert Bei den Nachkommen wird überprüft, ob das fremde genetische Material ins Genom integriert wurde Durch Inzucht solcher modifizierter Tiere wird eine neue, homozygote genetische Linie etabliert Einsatzgebiete genetische Information einbringen genetische Information zerstören Verwendung als Lebend-Bioreaktor Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 7
8 Transgene Tiere Durch Wahl geeigneter Promotoren läßt sich der Ort der Genexpression steuern z.b.: ß-Casein Promotor Immunglobulin-Promotor... Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 8
9 Methodenspektrum Transgene Tiere Gentransfer mittels retroviraler Vektoren Mikroinjektion von DNA Transfektion embyonaler Stammzellen Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 9
10 Transgene Tiere - Transfektion embryonaler Stammzellen Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 10
11 Transgene Tiere - retroviraler Gentransfer Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 11
12 Transgene Pflanzen - wie? Bestimmte Bakterienarten können Pflanzen infizieren Agrobacterium tumefaciens Ti-Plasmid (tumor inducing) Agrobacterium rhizogenes Ri-Plasmid (root inducing) "entwaffnete" Ti Plasmide werden zum Gentransfer eingesetzt Pathogenitätsgene wurden entfernt enthalten sind: DNA-Abschnitte für die Integration ins Wirtsgenom Selektionsmarker Fremdgen Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 12
13 Transgene Pflanzen - wie? Blattstücke werden mit Suspension rekombinanter Agrobakterium- Zellen inkubiert Auf einem Medium mit geeigneter Hormonzugabe wird Sproßbildung induziert Bakterien werden mit Antibiotikum abgetötet Transformierte Pflanzen(zellen) werden positiv selektioniert Wurzelbildung wird hormonell induziert ganze Pflanzen werden regeneriert geht nur in dikotylen Pflanzen gut Getreide, Mais, Reis sind monokotyl direkter Gentransfer mittels Gene Gun Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 13
14 Transgene Pflanzen - was wird verbessert? Resistenz gegen Schädlinge Viren Pilze Insekten Resistenz gegen Pflanzenschutzmittel Verbesserung der Pflanzenqualität Fettsäurespektrum im Raps Aminosäurezusammensetzung der Proteine Anti-Matsch Paradeiser Stärke-Qualität und Gehalt bei Erdäpfeln Produktion von Fremdprotein Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 14
15 Optimierungsmöglichkeiten Codon usage Datenbank: Kopienzahl ( Amplifikation ) Integrationsort Regulation stärkerer Promoter schwächerer Promoter dichterer Promoter nicht nur die kodierende Sequenz ist wichtig, auch die Umgebung, z.b.: Kozak sequence in Eukaryonten :GCCGCCPuCCAUGG Sekundärstruktur der mrna Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 15
16 PCR Überblick Polymerase Chain Reaction Grundlagen, Komponenten Enzyme fidelity quantative PCR, real-time PCR alternative DNA- und RNA- Amplifikationsmethoden Hauptanwendungsgebiete: Diagnostik: Nachweis von Krankheitserregern, Mutationen, Genexpression, Identität von Individuen Gentechnik: extrem wichtiges Hilfsmittel beim Klonieren Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 16
17 PCR Exponentielle Amplifikation E = b * 2 n E= Zahl an gebildeten Molekülen b= Ausgangszahl von Molekülen n= Zahl der PCR Zyklen Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 17
18 PCR Reagenzien Template (DNA oder RNA) 2 Primer dntps PCR Puffer und: thermostabile DNA Polymerase (Taq Polymerase) vom thermophilen Mikroorganismus Thermus aquaticus Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 18
19 PCR Prinzip Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 19
20 Vergleich von 2 wichtigen thermostabilen DNA Polymerasen Taq Exonuklease 5'-3 Ja 3-5' Nein Reverse Transcriptase Aktivität schwach entstehende DNA Enden 3'A Pfu Nein Ja n.a. Blunt Taq: Thermus aquaticus Pfu: Pyrococcus furiosus (proofreading Aktivität!) zahlreiche andere thermostabile DNA Polymerasen stehen zur Verfügung reverse Transkriptase Aktivität nur unter speziellen Pufferbedingungen (z.b. Mangan statt Magnesium) Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 20
21 Design von PCR-Primern meistens Nukleotide lang "uniqueness" am besten mit Computerprogramm überprüfen besonders am 3' Ende des Primers muß die Basenpaarung optimal sein 5' die Basen sollten zufällig verteilt sein, der G+C Gehalt möglichst nicht extrem lange A+T bzw. G+C Abschnitte wenn möglich vermeiden interne Sekundärstruktur minimieren 3' Verlängerung durch Polymerase möglich! Beispiel für ein Computerprogramm zum Primerdesign: Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 21
22 Design von PCR-Primern die 2 Primer sollten zueinander möglichst wenig komplementär sein 5' Primer 1 vs. Primer 1, Primer 2 vs. Primer 2, Primer 1 vs. Primer 2 3' 5' 3' 5' 3' 5' 3' 5' die Annealingtemperatur der beiden Primer sollte möglichst gleich sein, weniger als 3 Unterschied ideal am 5' Ende der Primer können lange (bis zu etwa 30 Basen), nichtkomplementäre Sequenzen angehängt werden, um z.b. Restriktionsstellen an das PCR Produkt anzufügen 3' 5' 3' Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 22
23 Schmelztemperatur T m durch Hitze "schmelzen" die Wasserstoffbrückenbindungen zwischen den Basenpaaren T m ist die Temperatur, bei der die Hälfte der DNA Stränge als Einzelstrang und die andere Hälfte als Doppelstrang vorliegt T m ist abhängig von der Länge und der Basenzusammensetzung der DNA: mehr Basen und/oder ein höherer Gehalt an G und C bedeutet höhere T m, weil: einfache Faustformel für T m von kurzen Oligos 4 C für jedes G C Basenpaar 2 C für jedes A T Basenpaar Tm G C > Tm A T für längere Oligos: Computerprogramm für T m verwenden! ungefähr: T anneal wird ca. 4 C unter T m gewählt Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 23
24 Diagnostische Anwendung der PCR Mit normaler PCR bekommt man sehr leicht und schnell ein qualitatives Ergebnis, d.h. z.b. eine Antwort auf die Frage ist ein bestimmer Krankheitserreger im Probematerial enthalten?. Eine quantitative Aussage, also wieviele Viruspartikel, wieviel mrna, etc. ist allerdings nicht möglich. Das wird klar, wenn man sich die Bildung von PCR Produkt während einer PCR Reaktion ansieht. PCR-Produktbildung in Abhängigkeit von der Templatemenge Menge an PCR Produkt Ausgangsmenge an Template PCR Zyklus Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 24
25 Daraus folgt: Quantitative PCR darf nicht primär nur die Menge an Endprodukt untersuchen, sondern muß genau verfolgen, wann das Produkt gebildet wird. Also: wieviel mit wann kombinieren Produktmenge unterhalb der Nachweisgrenze Diagnostische Anwendung der PCR Menge an PCR Produkt # PCR Zyklus d.h. man muß während der gesamten PCR beobachten, was passiert! Ausgangsmenge an Template Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 25
26 Real-time PCR (RT-PCR) - quantitative PCR präzise, high-throughput, und relativ leicht durchführbar Quantifizierung der Reaktionsprodukte bei jedem einzelnen PCR Zyklus. Sehr breiter dynamischer Bereich: ca fach Alle real-time PCR Systeme basieren auf der Detektion und Quantifizierung eines fluoreszierenden Reporters, dessen Signal direkt proportional mit der Mange an gebildetem PCR Produkt ist. Im einfachsten Format verwendet man einen für DNA spezifischen Farbstoff, SYBR Green (sprich: Seiber Grien). SYBR Green bindet an doppelsträngige DNA, und fluoresziert im gebundenen Zustand nach Anregung mit Licht entsprechender Wellenlänge. Mit zunehmender Menge an PCR Produkt nimmt die beobachtete Fluoreszenz zu. Vorteile von SYBR Green: billig, sensitiv, einfach zu verwenden. Nachteil: bindet an jeden DNA-Doppelstrang, also auch z.b. an Primer- Dimere, und an unspezifische, falsche PCR Produkte. Gutes Design der Primer und geeignete Kontrollreaktionen unbedingt nötig! Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 26
27 Dideoxy DNA Sequenzierung - was ist ein ddntp? dd = dideoxy die Methode wurde von Fred Sanger entwickelt Sanger F, Nicklen S, Coulson AR. Proc Natl Acad Sci U S A Dec;74(12): DNA sequencing with chain-terminating inhibitors. 5' 4' Deoxy 3' um die Elongation des DNA-Strangs zu verhindern; kann keine Phosphodiesterbindung mit einem dntp bilden 2' 1' Deoxy (weil es DNA ist!) Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 27
28 DNA Sequenzierung - Animationen Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 28
29 DNA Sequenzierung Wie die DNA nach der Sequenzierungsreaktion sichtbar gemacht wird: DNA Polymerase dntps (100µM) früher: radioaktive Markierung von Primer oder den eingebauten Nukleotiden verwendete Isotope: 35 S, 32 P heute: Fluoreszenz-Markierung der Dideoxynucleotide für jedes der 4 ddntps wird eine andere Farbe (also ein anderer Fluoreszenzfarbstoff) verwendet +ddatp (1µM) +ddgtp (1µM) +ddttp (1µM) A G T C +ddctp (1µM) A G T C A G T C Gemisch von Reaktionsprodukten, die sich in der Länge um jeweils 1 Base unterscheiden. Die letzte Base trägt dabei jeweils den spezifischen Fluoreszenzfarbstoff. Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 29
30 DNA Sequenzierung - Elektrophorese Gele in Kapillaren (oder, in älteren Geräten, flach zwischen Glasplatten Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 30
31 DNA Sequenzierung - Auswertung Jedes der 4 ddntps ist mit einem anderen Farbstoff markiert Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 31
32 Microarrays Was sind DNA arrays oder Microarrays? Array: Aufstellung, Ansammlung (militärisch) DNA arrays bestehen aus einer großen Anzahl regelmäßig und systematisch aufgebrachter (aufgespotteter; spot = Punkt, Fleck) DNA Moleküle auf einem festen Träger (Nylon Membran, Glasplättchen, Silicon chip). Ein Spot enthält in der Regel nur eine Art (Sequenz) von DNA. Der Durchmesser der Spots in microarrays ist meist kleiner als 250 µm). Hunderte bis viele Tausend solcher Spots gemeinsam bilden einen Array. Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 32
33 Microarrays Hauptsächlich kommen 2 Arten von DNA arrays zur Anwendung: 1. Oligonucleotid Microarrays oder oligo chip. Bei den immobilisierten DNA Molekülen handelt es sich um Oligonukleotide mit einer Länge von etwa 20 bis 30 Basen. 2. cdna Microarrays oder cdna chip. cdna oder (meist mit PCR amplifizierte cdna) wird immobilisiert. Die Länge der cdna Stücke ist meist kleiner als 2000 bp. 3. Selten kommen auch Genomische Microarrays oder genomic chips zum Einsatz. Hier werden genomische DNA Abschnitte mit einer Länge mehrerer kbp immobilisiert. Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 33
34 Was macht man mit DNA Arrays? Microarrays Das Hauptziel ist meist, Information über die Expression von Genen in bestimmen Geweben, Zellen, etc. zu gewinnen. Z.B.: welche Gene werden in einem bestimmten Gewebe exprimiert oder nicht exprimiert, welche Gene werden unter bestimmten Einflüssen hinauf- oder hinunterreguliert. Man untersucht z.b.: verschiedene Gewebe eines Organismus verschiedene Entwicklungsstadien alt - jung verschiedene Genotypen krank - gesund verschiedene Behandlungen verschiedene Zeiten nach einer Behandlung Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 34
35 Microarrays Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 35
36 Blotting Techniken Southern Blot: DNA auf Filter immobilisiert, Detektion mit markierter DNA oder RNA Sonde (probe). J Mol Biol 1975 Nov 5;98(3): Detection of specific sequences among DNA fragments separated by gel electrophoresis. Edward M. Southern Northern Blot: RNA auf Filter immobilisiert Western Blot: Protein auf Filter immobilisiert, Detektion mit spezifischem Antikörper Markierung: radioaktiv: P 32, S 35 nicht-radioaktiv: DIG (Digoxigenin, Roche), Biotin-Streptavidin Markierung Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 36
37 Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 37
38 Prinzip Southern Blots macht man, um komplementäre DNA Sequenzen mit spezifischen Sonden nach Auftrennung mittels Elektrophorese zu detektieren. Northern Blots sind eine Variation des Southern Blots. Beim Northern wird nicht DNA sondern RNA elektrophoretisch aufgetrennt und dann mit spezifischen Sonden detektiert. Im Gegensatz zu einer unspezifischen Färbung (z.b. mit Ethidiumbromid) werden nur die spezifischen Banden sichtbar gemacht. Damit die DNA Banden während der Hybrisidierung nicht davonschwimmen immoblisiert man sie auf einer Membran aus Nylon oder Nitrozellulose. Molekularbiologie für AW, VO , SS 2007, J. Glößl, Teil 3 38
Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR)
 PCR Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR) von Kary B. Mullis entwickelt (1985) eigentlich im Mai 1983 bei einer nächtlichen Autofahrt erstes erfolgreiches Experiment am 16.12.1983
PCR Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR) von Kary B. Mullis entwickelt (1985) eigentlich im Mai 1983 bei einer nächtlichen Autofahrt erstes erfolgreiches Experiment am 16.12.1983
Transgene Organismen
 Transgene Organismen Themenübersicht 1) Einführung 2) Komplementäre DNA (cdna) 3) Vektoren 4) Einschleusung von Genen in Eukaryontenzellen 5) Ausmaß der Genexpression 6) Genausschaltung (Gen-Knockout)
Transgene Organismen Themenübersicht 1) Einführung 2) Komplementäre DNA (cdna) 3) Vektoren 4) Einschleusung von Genen in Eukaryontenzellen 5) Ausmaß der Genexpression 6) Genausschaltung (Gen-Knockout)
Medizinische Fakultät Auswertestrategien von Microarrays Einführung
 Medizinische Fakultät Auswertestrategien von Microarrays Einführung PD Dr. Knut Krohn IZKF Leipzig Dr. Markus Eszlinger Med. Klinik III Forschungslabor DNA RNA Hintergrund Charakteristisches Muster der
Medizinische Fakultät Auswertestrategien von Microarrays Einführung PD Dr. Knut Krohn IZKF Leipzig Dr. Markus Eszlinger Med. Klinik III Forschungslabor DNA RNA Hintergrund Charakteristisches Muster der
SCRIPTUM HIGH PRECISE
 Nur für Forschungszwecke Datenblatt Artikel BS.50.020 = 20 Reaktionen x 50 µl Artikel BS.50.100 = 100 Reaktionen x 50 µl Artikel BS.50. 500 = 500 Reaktionen x 50 µl Haltbarkeit: 12 Monate Lagerung bei
Nur für Forschungszwecke Datenblatt Artikel BS.50.020 = 20 Reaktionen x 50 µl Artikel BS.50.100 = 100 Reaktionen x 50 µl Artikel BS.50. 500 = 500 Reaktionen x 50 µl Haltbarkeit: 12 Monate Lagerung bei
PCR. Inhalt. Was ist PCR? Eine Definition. Was ist PCR? Eine Definition. Was ist PCR? Eine Definition. Was ist PCR?
 Inhalt Was ist? Eine Definition Optimierung Anwendungsgebiete - in der Gentechnologie - in der Diagnostik Zusammenfassung von Christian Jogler (Abteilung für Mol. & Med. Virologie) Was ist? Eine Definition
Inhalt Was ist? Eine Definition Optimierung Anwendungsgebiete - in der Gentechnologie - in der Diagnostik Zusammenfassung von Christian Jogler (Abteilung für Mol. & Med. Virologie) Was ist? Eine Definition
1. PCR Polymerase-Kettenreaktion
 entechnische Verfahren 1. PCR Polymerase-Kettenreaktion Die PCR (engl. Polymerase Chain Reaction) ist eine Methode, um die DNA zu vervielfältigen, ohne einen lebenden Organismus, wie z.b. Escherichia coli
entechnische Verfahren 1. PCR Polymerase-Kettenreaktion Die PCR (engl. Polymerase Chain Reaction) ist eine Methode, um die DNA zu vervielfältigen, ohne einen lebenden Organismus, wie z.b. Escherichia coli
Inhalt. 3 Das Werkzeug... 47 3.1 Restriktionsenzyme... 47 3.2 Gele... 58 3.2.1 Agarosegele... 58
 Inhalt 1 Was ist denn Molekularbiologie, bitteschön?...................... 1 1.1 Das Substrat der Molekularbiologie, oder: Molli-World für Anfänger.... 2 1.2 Was brauche ich zum Arbeiten?..................................
Inhalt 1 Was ist denn Molekularbiologie, bitteschön?...................... 1 1.1 Das Substrat der Molekularbiologie, oder: Molli-World für Anfänger.... 2 1.2 Was brauche ich zum Arbeiten?..................................
Cornel Mülhardt. Genomics. 6. Auflaqe. Spektrum k - / l AKADEMISCHER VERLAG
 I Cornel Mülhardt Genomics 6. Auflaqe Spektrum k - / l AKADEMISCHER VERLAG Inhalt 1 Was ist denn "Molekularbiologie", bitteschön? 1 1.1 Das Substrat der Molekularbiologie, oder: Molli-World für Anfänger...
I Cornel Mülhardt Genomics 6. Auflaqe Spektrum k - / l AKADEMISCHER VERLAG Inhalt 1 Was ist denn "Molekularbiologie", bitteschön? 1 1.1 Das Substrat der Molekularbiologie, oder: Molli-World für Anfänger...
DNA Sequenzierung. Transkriptionsstart bestimmen PCR
 10. Methoden DNA Sequenzierung Transkriptionsstart bestimmen PCR 1. Erklären Sie das Prinzip der Sanger Sequenzierung. Klären Sie dabei folgende Punkte: a) Welche besondere Art von Nukleotiden wird verwendet
10. Methoden DNA Sequenzierung Transkriptionsstart bestimmen PCR 1. Erklären Sie das Prinzip der Sanger Sequenzierung. Klären Sie dabei folgende Punkte: a) Welche besondere Art von Nukleotiden wird verwendet
Thema Gentechnologie. Erwin R. Schmidt Institut für Molekulargenetik Gentechnologische Sicherheitsforschung & Beratung
 Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik Gentechnologische Sicherheitsforschung & Beratung Die Genklonierung in Bakterien Vektor-DNA Spender-DNA Restriktionsenzym Rekombinante
Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik Gentechnologische Sicherheitsforschung & Beratung Die Genklonierung in Bakterien Vektor-DNA Spender-DNA Restriktionsenzym Rekombinante
Prüfungsfragenkatalog für für Grundlagen der Gentechnik und Biotechnologie (Prof. Prof. Rudolf Bauer und Prof. Karin Ardjomand-Wölkart)
 Prüfungsfragenkatalog für für Grundlagen der Gentechnik und Biotechnologie (Prof. Prof. Rudolf Bauer und Prof. Karin Ardjomand-Wölkart) Stand: September 2014 Termin: 29.09.2014 1. Was ist Western Blot?
Prüfungsfragenkatalog für für Grundlagen der Gentechnik und Biotechnologie (Prof. Prof. Rudolf Bauer und Prof. Karin Ardjomand-Wölkart) Stand: September 2014 Termin: 29.09.2014 1. Was ist Western Blot?
Molekularbiologie/ Genomics
 Cornel Mülhardt Molekularbiologie/ Genomics 5. Auflage ELSEVIER SPEKTRUM AKADEMISCHER VERLAG Spektrum k-zlakademischer VERLAG Inhalt 1 Was ist denn "Molekularbiologie", bitteschön? 1 1.1 Das Substrat der
Cornel Mülhardt Molekularbiologie/ Genomics 5. Auflage ELSEVIER SPEKTRUM AKADEMISCHER VERLAG Spektrum k-zlakademischer VERLAG Inhalt 1 Was ist denn "Molekularbiologie", bitteschön? 1 1.1 Das Substrat der
PCR (polymerase chain reaction)
 PCR (polymerase chain reaction) Ist ein in vitro Verfahren zur selektiven Anreicherung von Nukleinsäure-Bereichen definierter Länge und definierter Sequenz aus einem Gemisch von Nukleinsäure-Molekülen
PCR (polymerase chain reaction) Ist ein in vitro Verfahren zur selektiven Anreicherung von Nukleinsäure-Bereichen definierter Länge und definierter Sequenz aus einem Gemisch von Nukleinsäure-Molekülen
Transcriptomics: Analysis of Microarrays
 Transcriptomics: Analysis of Microarrays Dion Whitehead dion@uni-muenster.de Division of Bioinformatics, Westfälische Wilhelms Universität Münster Microarrays Vorlesungsüberblick : 1. Überblick von Microarray
Transcriptomics: Analysis of Microarrays Dion Whitehead dion@uni-muenster.de Division of Bioinformatics, Westfälische Wilhelms Universität Münster Microarrays Vorlesungsüberblick : 1. Überblick von Microarray
Funktionelle Genomik. praktische Anwendungen
 Funktionelle Genomik praktische Anwendungen Schmelzpunkt der DNA Einzelsträngige DNA absorbiert UV-Licht effektiver SYBR Green fluoresziert nur wenn es an doppelsträngiger DNA bindet Fluoreszenz erhöht
Funktionelle Genomik praktische Anwendungen Schmelzpunkt der DNA Einzelsträngige DNA absorbiert UV-Licht effektiver SYBR Green fluoresziert nur wenn es an doppelsträngiger DNA bindet Fluoreszenz erhöht
Klonierung von S2P Rolle der M19-Zellen. POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel
 Klonierung von S2P Rolle der M19-Zellen POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel Inhalt 1. Was ist eine humane genomische DNA-Bank? 2. Unterschied zwischen cdna-bank und genomischer DNA-Bank?
Klonierung von S2P Rolle der M19-Zellen POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel Inhalt 1. Was ist eine humane genomische DNA-Bank? 2. Unterschied zwischen cdna-bank und genomischer DNA-Bank?
'Agaroselels große DNA-Fragmente im Ethidiumbromid-gefärbten Agarosegel normalenrueise
 4. (Kap2-Enzyme) a) KleinJDNA-Fragmente haben weniger negative Ladungen als große, aber das Masse/Ladungs-Verhältnis ist gleich. Warum wandern sie trotzdem schneller in der Agarose- Gelelektrophorese?
4. (Kap2-Enzyme) a) KleinJDNA-Fragmente haben weniger negative Ladungen als große, aber das Masse/Ladungs-Verhältnis ist gleich. Warum wandern sie trotzdem schneller in der Agarose- Gelelektrophorese?
1. Erklären Sie das Prinzip der Sanger Sequenzierung. Klären Sie dabei folgende Punkte: a) Welche besondere Art von Nukleotiden wird verwendet und
 10. Methoden 1. Erklären Sie das Prinzip der Sanger Sequenzierung. Klären Sie dabei folgende Punkte: a) Welche besondere Art von Nukleotiden wird verwendet und welche Funktion haben diese bei der Sequenzierungsreaktion?
10. Methoden 1. Erklären Sie das Prinzip der Sanger Sequenzierung. Klären Sie dabei folgende Punkte: a) Welche besondere Art von Nukleotiden wird verwendet und welche Funktion haben diese bei der Sequenzierungsreaktion?
Alternative Methoden der RNA-Analyse
 Alternative Methoden der RNA-Analyse In diesem Versuch wurde die Northern Blot Hybridisierung zur Analyse isolierter mrna eingesetzt. Mit dieser Technik können Größe und Menge einer spezifischen RNA bestimmt
Alternative Methoden der RNA-Analyse In diesem Versuch wurde die Northern Blot Hybridisierung zur Analyse isolierter mrna eingesetzt. Mit dieser Technik können Größe und Menge einer spezifischen RNA bestimmt
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr
 Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
Produktkatalog 2010. Molekularbiologische Reagenzien
 Produktion, Vertrieb und Serviceleistung im Bereich der Molekularbiologie und Medizin Produktkatalog 2010 Molekularbiologische Reagenzien Molegene GmbH Bienenweg 28 35764 Sinn Tel. 02772-570952 Fax 02772-570945
Produktion, Vertrieb und Serviceleistung im Bereich der Molekularbiologie und Medizin Produktkatalog 2010 Molekularbiologische Reagenzien Molegene GmbH Bienenweg 28 35764 Sinn Tel. 02772-570952 Fax 02772-570945
II. GENOMIK: GLEICHZEITIGE UNTERSUCHUNG VON MEHREREN MAKROMOLEKÜLEN
 II. GENOMIK: GLEICHZEITIGE UNTERSUCHUNG VON MEHREREN MAKROMOLEKÜLEN Strukturelle Genomik Genomische Bibliothek, EST Datenbank DNA-Sequenzierung Genomprogramme Polymorphismen RFLP Herstellung einer DNA-Bibliothek
II. GENOMIK: GLEICHZEITIGE UNTERSUCHUNG VON MEHREREN MAKROMOLEKÜLEN Strukturelle Genomik Genomische Bibliothek, EST Datenbank DNA-Sequenzierung Genomprogramme Polymorphismen RFLP Herstellung einer DNA-Bibliothek
Einführung in die Bioinformatik
 Einführung in die Bioinformatik Kay Nieselt SS 011 9. It s hip to chip - von Microarrays zu personalisierter Medizin WSI/ZBIT, Eberhard Karls Universität Tübingen Das menschliche Genom (.000.000.000 Basenpaare)
Einführung in die Bioinformatik Kay Nieselt SS 011 9. It s hip to chip - von Microarrays zu personalisierter Medizin WSI/ZBIT, Eberhard Karls Universität Tübingen Das menschliche Genom (.000.000.000 Basenpaare)
Molekularbiologische Methoden
 Molekularbiologische Methoden im Lebensmittel-Labor Dr. rer. nat. Armin Pahl LADR GmbH MVZ Dr. Kramer & Kollegen 04152 803-0 www.ladr.de DNA 1866 Gregor Mendel veröffentlicht seine Versuche über Pflanzen-Hybriden,
Molekularbiologische Methoden im Lebensmittel-Labor Dr. rer. nat. Armin Pahl LADR GmbH MVZ Dr. Kramer & Kollegen 04152 803-0 www.ladr.de DNA 1866 Gregor Mendel veröffentlicht seine Versuche über Pflanzen-Hybriden,
Grundideen der Gentechnik
 Grundideen der Gentechnik Die Gentechnik kombiniert Biotechnik und Züchtung. Wie in der Züchtung wird die Erbinformation eines Lebewesen verändert. Dabei nutzte man in den Anfängen der Gentechnik vor allem
Grundideen der Gentechnik Die Gentechnik kombiniert Biotechnik und Züchtung. Wie in der Züchtung wird die Erbinformation eines Lebewesen verändert. Dabei nutzte man in den Anfängen der Gentechnik vor allem
PCR basierte- Detektionstechniken
 PCR basierte- Detektionstechniken Warum überhaupt? Forensische Analysen: Vaterschaftstests, Kriminalistik Mikrobielle Gemeinschaften: Biofilme, medizinische Mikrobiologie 2 Warum überhaupt? minimale Mengen
PCR basierte- Detektionstechniken Warum überhaupt? Forensische Analysen: Vaterschaftstests, Kriminalistik Mikrobielle Gemeinschaften: Biofilme, medizinische Mikrobiologie 2 Warum überhaupt? minimale Mengen
Forschungszentrum Karlsruhe
 Forschungszentrum Karlsruhe in der Helmholtz-Gemelnschaft Wissenschaftliche Berichte FZKA7106 Biochemische Charakterisierung der Isoprensynthase aus der Graupappel (Populus x canescens (Ait.) Sm.) und
Forschungszentrum Karlsruhe in der Helmholtz-Gemelnschaft Wissenschaftliche Berichte FZKA7106 Biochemische Charakterisierung der Isoprensynthase aus der Graupappel (Populus x canescens (Ait.) Sm.) und
Sequenzierung. Aufklärung der Primärstruktur von DNA. Biotechnik Kurs WS 2006/07
 Sequenzierung Aufklärung der Primärstruktur von DNA Biotechnik Kurs WS 2006/07 AK Engels Angelika Keller Übersicht Geschichtlicher Hintergrund Maxam-Gilbert Sequenzierung Sanger Sequenzierung Neuere Sequenzierungstechnologien
Sequenzierung Aufklärung der Primärstruktur von DNA Biotechnik Kurs WS 2006/07 AK Engels Angelika Keller Übersicht Geschichtlicher Hintergrund Maxam-Gilbert Sequenzierung Sanger Sequenzierung Neuere Sequenzierungstechnologien
Untersuchungen zur differenziellen Genexpression im ZNS von Noradrenalintransporter-Knockout- und Wildtyp-Mäusen
 Untersuchungen zur differenziellen Genexpression im ZNS von Noradrenalintransporter-Knockout- und Wildtyp-Mäusen Inaugural-Dissertation zur Erlangung des Doktorgrades (Dr. rer. nat.) der Mathematisch-Naturwissenschaftlichen
Untersuchungen zur differenziellen Genexpression im ZNS von Noradrenalintransporter-Knockout- und Wildtyp-Mäusen Inaugural-Dissertation zur Erlangung des Doktorgrades (Dr. rer. nat.) der Mathematisch-Naturwissenschaftlichen
Inhalt 1 Modellorganismen
 Inhalt 1 Modellorganismen....................................... 1 1.1 Escherichia coli....................................... 1 1.1.1 Historisches...................................... 3 1.1.2 Lebenszyklus.....................................
Inhalt 1 Modellorganismen....................................... 1 1.1 Escherichia coli....................................... 1 1.1.1 Historisches...................................... 3 1.1.2 Lebenszyklus.....................................
Genomsequenzierung für Anfänger
 Genomsequenzierung für Anfänger Philipp Pagel 8. November 2005 1 DNA Sequenzierung Heute wird DNA üblicherweise mit der sogenannten Sanger (oder chain-terminationoder Didesoxy-) Methode sequenziert dessen
Genomsequenzierung für Anfänger Philipp Pagel 8. November 2005 1 DNA Sequenzierung Heute wird DNA üblicherweise mit der sogenannten Sanger (oder chain-terminationoder Didesoxy-) Methode sequenziert dessen
Regulation der Genexpression: regulierbare Promotoren, Proteine und sirna
 Regulation der Genexpression: regulierbare Promotoren, Proteine und sirna Biochemie Praktikum Christian Brendel, AG Grez Ebenen der Genregulation in Eukaryoten Cytoplasma DNA Zellkern Introns Exons Chromatin
Regulation der Genexpression: regulierbare Promotoren, Proteine und sirna Biochemie Praktikum Christian Brendel, AG Grez Ebenen der Genregulation in Eukaryoten Cytoplasma DNA Zellkern Introns Exons Chromatin
Die DNA Replikation. Exakte Verdopplung des genetischen Materials. Musterstrang. Neuer Strang. Neuer Strang. Eltern-DNA-Doppelstrang.
 Die DNA Replikation Musterstrang Neuer Strang Eltern-DNA-Doppelstrang Neuer Strang Musterstrang Exakte Verdopplung des genetischen Materials Die Reaktion der DNA Polymerase 5`-Triphosphat Nächstes Desoxyribonucleosidtriphosphat
Die DNA Replikation Musterstrang Neuer Strang Eltern-DNA-Doppelstrang Neuer Strang Musterstrang Exakte Verdopplung des genetischen Materials Die Reaktion der DNA Polymerase 5`-Triphosphat Nächstes Desoxyribonucleosidtriphosphat
Molekularbiologische / gentechnische Methoden
 Molekularbiologische / gentechnische Methoden MPM 1 Wie lässt sich ein spezifisches Gen/Genprodukt molekular analysieren? Fundamentales Problem: Komplexität biologischer Systeme MPM 2 Ein Ausschnitt aus
Molekularbiologische / gentechnische Methoden MPM 1 Wie lässt sich ein spezifisches Gen/Genprodukt molekular analysieren? Fundamentales Problem: Komplexität biologischer Systeme MPM 2 Ein Ausschnitt aus
Warum man nicht schon in der SDS- Page eine Immunfärbung machen kann. Warum bei A-Tailingzyklus die A s nich immer mehr werden
 Molbi Nachklausur 2009 Hier mal so die Fragen die mir noch so einfallen. Also es war gefragt: Warum man nicht schon in der SDS- Page eine Immunfärbung machen kann. Warum bei A-Tailingzyklus die A s nich
Molbi Nachklausur 2009 Hier mal so die Fragen die mir noch so einfallen. Also es war gefragt: Warum man nicht schon in der SDS- Page eine Immunfärbung machen kann. Warum bei A-Tailingzyklus die A s nich
Das Prinzip der DNA-Sequenzierung Best.- Nr. 201.3055
 Das Prinzip der DNA-Sequenzierung Best.- Nr. 201.3055 Allgemeine Informationen Prinzip der DNA-Sequenzierung Ziel dieses Versuchs ist einen genauen Überblick über die Verfahrensweise der DNA- Sequenzierung
Das Prinzip der DNA-Sequenzierung Best.- Nr. 201.3055 Allgemeine Informationen Prinzip der DNA-Sequenzierung Ziel dieses Versuchs ist einen genauen Überblick über die Verfahrensweise der DNA- Sequenzierung
A- Zugabe von 180µl Pufferlösung und Proteinase K, Inkubation bei 56 C. B- Zugabe von 200µl einer zweiten Pufferlösung, Inkubation bei 70 C
 3 Methoden 3.1 Extraktion der DNA aus den Paraffinschnitten 3.1.1 Extraktions-Kit Das QIAamp DNA Mini Kit- System beruht auf dem Prinzip der Auflösung der Eiweiße mit Proteinase K, DNA Bindung an eine
3 Methoden 3.1 Extraktion der DNA aus den Paraffinschnitten 3.1.1 Extraktions-Kit Das QIAamp DNA Mini Kit- System beruht auf dem Prinzip der Auflösung der Eiweiße mit Proteinase K, DNA Bindung an eine
Expression der genetischen Information Skript: Kapitel 5
 Prof. A. Sartori Medizin 1. Studienjahr Bachelor Molekulare Zellbiologie FS 2013 12. März 2013 Expression der genetischen Information Skript: Kapitel 5 5.1 Struktur der RNA 5.2 RNA-Synthese (Transkription)
Prof. A. Sartori Medizin 1. Studienjahr Bachelor Molekulare Zellbiologie FS 2013 12. März 2013 Expression der genetischen Information Skript: Kapitel 5 5.1 Struktur der RNA 5.2 RNA-Synthese (Transkription)
Sequenzierung. Sequenzierung. DNA in den letzten 50 Jahren. Warum Sequenzierung
 Sequenzierung von Thomas Grunwald Abteilung für Med. und Mol. Virologie Sequenzierung Hintergrund Allgemeiner Überblick Funktionsweise der Sequenzierung Sequenzierungsprotokoll Auswertung der Daten Probleme
Sequenzierung von Thomas Grunwald Abteilung für Med. und Mol. Virologie Sequenzierung Hintergrund Allgemeiner Überblick Funktionsweise der Sequenzierung Sequenzierungsprotokoll Auswertung der Daten Probleme
Methoden der Gentechnik
 Methoden der Gentechnik *** DNA-Rekombination und Klonierung *** 1. Allgemeine Grundprinzipien 1.1. Wesen der Gentechnik 1.2. Allgemeine Ziele der Gentechnik 1.3. Molekulare Voraussetzungen 1.4. Wichtige
Methoden der Gentechnik *** DNA-Rekombination und Klonierung *** 1. Allgemeine Grundprinzipien 1.1. Wesen der Gentechnik 1.2. Allgemeine Ziele der Gentechnik 1.3. Molekulare Voraussetzungen 1.4. Wichtige
F-I Molekulare Zoologie: Teil I: Expressionsanalysen. Expressionsanalyse mittels RT-PCR
 F-I Molekulare Zoologie: Teil I: Expressionsanalysen Expressionsanalyse mittels RT-PCR Inhalt: Seite I. Generelles 1 II. RNA-Aufreinigung mit EZNA Total RNA Kit (PeqLab)...2 III. Umschreiben von RNA in
F-I Molekulare Zoologie: Teil I: Expressionsanalysen Expressionsanalyse mittels RT-PCR Inhalt: Seite I. Generelles 1 II. RNA-Aufreinigung mit EZNA Total RNA Kit (PeqLab)...2 III. Umschreiben von RNA in
Vorlesung LV-Nr. 954.104. Molekularbiologie für Agrarwissenschaften. J. Glößl, SS 2007
 Vorlesung LV-Nr. 954.104 Molekularbiologie für Agrarwissenschaften J. Glößl, SS 2007 Thematik: Molekularbiologische Methoden Teil 1 Die ppt Folien wurden freundlicherweise von Prof. Florian Rüker aus der
Vorlesung LV-Nr. 954.104 Molekularbiologie für Agrarwissenschaften J. Glößl, SS 2007 Thematik: Molekularbiologische Methoden Teil 1 Die ppt Folien wurden freundlicherweise von Prof. Florian Rüker aus der
Etablierung einer. Homemade - PCR
 Etablierung einer Homemade - PCR Anja Schöpflin Institut für Pathologie Universitätsklinikum Freiburg Überblick: Anwendungsgebiete der PCR Anforderungen an Primer Auswahl geeigneter Primer / Primerdesign
Etablierung einer Homemade - PCR Anja Schöpflin Institut für Pathologie Universitätsklinikum Freiburg Überblick: Anwendungsgebiete der PCR Anforderungen an Primer Auswahl geeigneter Primer / Primerdesign
Informationsveranstaltung Heimtierfuttermittel. PCR-Analytik zur Bestimmung von GVOs in Heimtierfuttermitteln. C. Haldemann, ALP
 Informationsveranstaltung Heimtierfuttermittel PCR-Analytik zur Bestimmung von GVOs in Heimtierfuttermitteln C. Haldemann, ALP Grundidee des Nachweises von GVOs mittels PCR Die Bestimmung genveränderter
Informationsveranstaltung Heimtierfuttermittel PCR-Analytik zur Bestimmung von GVOs in Heimtierfuttermitteln C. Haldemann, ALP Grundidee des Nachweises von GVOs mittels PCR Die Bestimmung genveränderter
Bayerische Landesanstalt für Landwirtschaft. Institut für Pflanzenschutz Luitgardis Seigner
 Bayerische Landesanstalt für Landwirtschaft Institut für Pflanzenschutz Luitgardis Seigner Schaderregernachweis mit der Polymerase-Kettenreaktion (PCR) Schaderregernachweis mit der Polymerase- Kettenreaktion
Bayerische Landesanstalt für Landwirtschaft Institut für Pflanzenschutz Luitgardis Seigner Schaderregernachweis mit der Polymerase-Kettenreaktion (PCR) Schaderregernachweis mit der Polymerase- Kettenreaktion
GVO Analyse-Methoden Theorie und Praxis Donau Soja Kongress Berlin, 07.05.15
 Genetic ID (Europe) GmbH 2015 GVO Analyse-Methoden Theorie und Praxis Donau Soja Kongress Berlin, 07.05.15 Genetic ID (Europe) GmbH Gegründet im Jahr 2001 Genetic ID NA das erste GVO-Testlabor in den USA
Genetic ID (Europe) GmbH 2015 GVO Analyse-Methoden Theorie und Praxis Donau Soja Kongress Berlin, 07.05.15 Genetic ID (Europe) GmbH Gegründet im Jahr 2001 Genetic ID NA das erste GVO-Testlabor in den USA
Polymerase-Kettenreaktion
 Polymerase-Kettenreaktion Universität für Bodenkultur Wien Interuniversitäres Department für Agrarbiotechnologie Tulln Ein Einblick über eine der wohl bekanntesten Analysemethoden der Neuzeit Martin Kellner
Polymerase-Kettenreaktion Universität für Bodenkultur Wien Interuniversitäres Department für Agrarbiotechnologie Tulln Ein Einblick über eine der wohl bekanntesten Analysemethoden der Neuzeit Martin Kellner
Zellbiologie: BSc Arbeiten 15/16
 Zellbiologie: BSc Arbeiten 15/16 Lehrstuhl Zellbiologie: Arbeitsgruppen Prof. Benedikt Kost Prof. Georg Kreimer PD Michael Lebert Slot Zeitraum Anzahl Plätze Semester 1 24.08.15 09.10.15 4 Ferien 2 09.11.15
Zellbiologie: BSc Arbeiten 15/16 Lehrstuhl Zellbiologie: Arbeitsgruppen Prof. Benedikt Kost Prof. Georg Kreimer PD Michael Lebert Slot Zeitraum Anzahl Plätze Semester 1 24.08.15 09.10.15 4 Ferien 2 09.11.15
Transgene Tiere: Genmodifikation in der Maus
 Transgene Tiere: Genmodifikation in der Maus Gentechnik und Genomics WiSe 2007/2008 Kristian M. Müller Institut für Biologie III Albert-Ludwigs-Universität Freiburg Nobelpreis Physiologie und Medizin 2007
Transgene Tiere: Genmodifikation in der Maus Gentechnik und Genomics WiSe 2007/2008 Kristian M. Müller Institut für Biologie III Albert-Ludwigs-Universität Freiburg Nobelpreis Physiologie und Medizin 2007
Transgene Tiere. Beispiele: - Das Gen für Wachstumshormon (GH) wurde mit einem starke Promotor in das Genom der Maus eingepflanzt.
 Transgene Tiere Definition: Ein transgenes Tier besitzt definierte Veränderungen im Genom, die nicht durch klassische Züchtung oder zufällige Mutagenese zu erreichen wären. Beispiele: - Das Gen für Wachstumshormon
Transgene Tiere Definition: Ein transgenes Tier besitzt definierte Veränderungen im Genom, die nicht durch klassische Züchtung oder zufällige Mutagenese zu erreichen wären. Beispiele: - Das Gen für Wachstumshormon
DNA-Sequenzierung. Martina Krause
 DNA-Sequenzierung Martina Krause Inhalt Methoden der DNA-Sequenzierung Methode nach Maxam - Gilbert Methode nach Sanger Einleitung Seit 1977 stehen zwei schnell arbeitende Möglichkeiten der Sequenzanalyse
DNA-Sequenzierung Martina Krause Inhalt Methoden der DNA-Sequenzierung Methode nach Maxam - Gilbert Methode nach Sanger Einleitung Seit 1977 stehen zwei schnell arbeitende Möglichkeiten der Sequenzanalyse
Transkriptionelle Repression als molekulare Grundlage der anti-inflammatorischen Wirkung von Glucocorticoiden
 Forschungszentrum Karlsruhe Technik und Umwelt Wissenschaftliche Berichte FZKA 6087 Transkriptionelle Repression als molekulare Grundlage der anti-inflammatorischen Wirkung von Glucocorticoiden Stefanie
Forschungszentrum Karlsruhe Technik und Umwelt Wissenschaftliche Berichte FZKA 6087 Transkriptionelle Repression als molekulare Grundlage der anti-inflammatorischen Wirkung von Glucocorticoiden Stefanie
Übung 11 Genregulation bei Prokaryoten
 Übung 11 Genregulation bei Prokaryoten Konzepte: Differentielle Genexpression Positive Genregulation Negative Genregulation cis-/trans-regulation 1. Auf welchen Ebenen kann Genregulation stattfinden? Definition
Übung 11 Genregulation bei Prokaryoten Konzepte: Differentielle Genexpression Positive Genregulation Negative Genregulation cis-/trans-regulation 1. Auf welchen Ebenen kann Genregulation stattfinden? Definition
5x QPCR Mix (ROX) Datenblatt. Artikel-Nr. BS µl Artikel-Nr. BS µl. (Nur für Forschung und in vitro-anwendungen)
 Datenblatt Artikel-Nr. BS76.520.0200 200 µl Artikel-Nr. BS76.520.1000 1.000 µl Artikel-Nr. BS76.520.5000 5.000 µl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
Datenblatt Artikel-Nr. BS76.520.0200 200 µl Artikel-Nr. BS76.520.1000 1.000 µl Artikel-Nr. BS76.520.5000 5.000 µl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
DNA Replikation ist semikonservativ. Abb. aus Stryer (5th Ed.)
 DNA Replikation ist semikonservativ Entwindung der DNA-Doppelhelix durch eine Helikase Replikationsgabel Eltern-DNA Beide DNA-Stränge werden in 5 3 Richtung synthetisiert DNA-Polymerasen katalysieren die
DNA Replikation ist semikonservativ Entwindung der DNA-Doppelhelix durch eine Helikase Replikationsgabel Eltern-DNA Beide DNA-Stränge werden in 5 3 Richtung synthetisiert DNA-Polymerasen katalysieren die
Stand von letzter Woche
 RUB ECR1 AXR1 Stand von letzter Woche E2 U? E1-like AXR1 Repressor ARF1 Proteasom AuxRE Repressor wird sehr schnell abgebaut notwendig für Auxinantwort evtl. Substrat für SCF Identifikation des SCF-Ubiquitin
RUB ECR1 AXR1 Stand von letzter Woche E2 U? E1-like AXR1 Repressor ARF1 Proteasom AuxRE Repressor wird sehr schnell abgebaut notwendig für Auxinantwort evtl. Substrat für SCF Identifikation des SCF-Ubiquitin
Dr. Jens Kurreck. Otto-Hahn-Bau, Thielallee 63, Raum 029 Tel.: 83 85 69 69 Email: jkurreck@chemie.fu-berlin.de
 Dr. Jens Kurreck Otto-Hahn-Bau, Thielallee 63, Raum 029 Tel.: 83 85 69 69 Email: jkurreck@chemie.fu-berlin.de Prinzipien genetischer Informationsübertragung Berg, Tymoczko, Stryer: Biochemie 5. Auflage,
Dr. Jens Kurreck Otto-Hahn-Bau, Thielallee 63, Raum 029 Tel.: 83 85 69 69 Email: jkurreck@chemie.fu-berlin.de Prinzipien genetischer Informationsübertragung Berg, Tymoczko, Stryer: Biochemie 5. Auflage,
Kursinhalte der Weiterbildung Molekulare Biotechnologie (MNr.: 237 / 0411 / 2010)
 Kursinhalte der Weiterbildung Molekulare Biotechnologie (MNr.: 237 / 0411 / 2010) Schwerpunkte im Bereich BIOANALYTIK Polyacrylamidelektrophorese von Nukleinsäuren im Vertikalsystem Agarosegelelektrophorese
Kursinhalte der Weiterbildung Molekulare Biotechnologie (MNr.: 237 / 0411 / 2010) Schwerpunkte im Bereich BIOANALYTIK Polyacrylamidelektrophorese von Nukleinsäuren im Vertikalsystem Agarosegelelektrophorese
Ektope Genexpression in Bakterien und Hefen
 Ektope Genexpression in Bakterien und Hefen Robert Jabulowsky AG Wels Methodenseminar BCII-Praktikum am Georg-Speyer-Haus 10.01. und 31.01.2012 Produktion von rekombinanten Proteinen = die gezielte Synthese
Ektope Genexpression in Bakterien und Hefen Robert Jabulowsky AG Wels Methodenseminar BCII-Praktikum am Georg-Speyer-Haus 10.01. und 31.01.2012 Produktion von rekombinanten Proteinen = die gezielte Synthese
Rekombinante Antikörper
 Frank Breitling und Stefan Dübel 2008 AGI-Information Management Consultants May be used for personal purporses only or by libraries associated to dandelon.com network. Rekombinante Antikörper Technische
Frank Breitling und Stefan Dübel 2008 AGI-Information Management Consultants May be used for personal purporses only or by libraries associated to dandelon.com network. Rekombinante Antikörper Technische
Rekombinante Wirkstoffe. Prof. Dr. Theo Dingermann Institut für Pharmazeutische Biologie Goethe-Universität Frankfurt Dingermann@em.uni-frankfurt.
 Rekombinante Wirkstoffe Prof. Dr. Theo Dingermann Institut für Pharmazeutische Biologie Goethe-Universität Frankfurt Dingermann@em.uni-frankfurt.de Praktische Definitionen Gentechnik Unmittelbare neukombination
Rekombinante Wirkstoffe Prof. Dr. Theo Dingermann Institut für Pharmazeutische Biologie Goethe-Universität Frankfurt Dingermann@em.uni-frankfurt.de Praktische Definitionen Gentechnik Unmittelbare neukombination
1. Nachschreibeklausur zur Vorlesung "Genetik" im WS 09/10 A. Matrikel-Nr.: Versuch: 1 2 3
 1. Nachschreibeklausur zur Vorlesung "Genetik" im WS 09/10 A Modul: Studiengang: Matrikel-Nr.: Versuch: 1 2 3 Vollständiger Name in Druckbuchstaben (Vorname Nachname): Jena, 01.04.2010, 10 12 Uhr; Unterschrift:
1. Nachschreibeklausur zur Vorlesung "Genetik" im WS 09/10 A Modul: Studiengang: Matrikel-Nr.: Versuch: 1 2 3 Vollständiger Name in Druckbuchstaben (Vorname Nachname): Jena, 01.04.2010, 10 12 Uhr; Unterschrift:
Genetik - The Human Genome Project. Überblick über die Genetik. Die gesamte Erbinformation eines Menschen befindet sich in jedem Zellkern
 Genetik - The Human Genome Project Überblick über die Genetik Die gesamte Erbinformation eines Menschen befindet sich in jedem Zellkern seines Körpers. 1 2 Im Organismus müsssen nun ständig Enzyme u. a.
Genetik - The Human Genome Project Überblick über die Genetik Die gesamte Erbinformation eines Menschen befindet sich in jedem Zellkern seines Körpers. 1 2 Im Organismus müsssen nun ständig Enzyme u. a.
Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers
 Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers FIGURE 20.1 Biology 6/e Biotechnologie Protein Expression Genomische DNA PCR Vektormolekül (Plasmid) Escherichia coli
Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers FIGURE 20.1 Biology 6/e Biotechnologie Protein Expression Genomische DNA PCR Vektormolekül (Plasmid) Escherichia coli
RUHR-UNIVERSITÄT BOCHUM
 RUHR-UNIVERSITÄT BOCHUM Fakultät für Chemie Titel der Lehreinheit (LE) Modulpraktika Biochemie im Schwerpunkt Molekulare Biologie und Biotechnologie der Pflanzen und Mikroorganismen Molekularbiologie von
RUHR-UNIVERSITÄT BOCHUM Fakultät für Chemie Titel der Lehreinheit (LE) Modulpraktika Biochemie im Schwerpunkt Molekulare Biologie und Biotechnologie der Pflanzen und Mikroorganismen Molekularbiologie von
DNA- Rekombinationstechnik. Gentechnik
 DNA- Rekombinationstechnik Gentechnik 1 Verwendung von Plasmiden in der Gentechnik Campbell 19.1 2 Die wichtigsten Schritte bei der DNA-Klonierung (Plasmid) Transformation 3 Durch Klonierung kann man DNA-Fragmente
DNA- Rekombinationstechnik Gentechnik 1 Verwendung von Plasmiden in der Gentechnik Campbell 19.1 2 Die wichtigsten Schritte bei der DNA-Klonierung (Plasmid) Transformation 3 Durch Klonierung kann man DNA-Fragmente
2) Veröffentlichungsnummer: PATENTANMELDUNG
 Europäisches Patentamt European Patent Office Dffice europeen des brevets 2) Veröffentlichungsnummer: 0 368 342 A2 EUROPAISCHE PATENTANMELDUNG 2) Anmeldenummer: 89120894.4 ) Anmeldetag: 10.11.89 it) Int.
Europäisches Patentamt European Patent Office Dffice europeen des brevets 2) Veröffentlichungsnummer: 0 368 342 A2 EUROPAISCHE PATENTANMELDUNG 2) Anmeldenummer: 89120894.4 ) Anmeldetag: 10.11.89 it) Int.
Klinische Chemie und Laboratoriumsmedizin Institut für MTA-Ausbildung am Klinikum Osnabrück
 Klinische Chemie und Laboratoriumsmedizin Institut für MTA-Ausbildung am Klinikum Osnabrück Polymerase-Kettenreaktion (PCR) Die Polymerase-Kettenreaktion (englisch Polymerase Chain Reaction, PCR) ist eine
Klinische Chemie und Laboratoriumsmedizin Institut für MTA-Ausbildung am Klinikum Osnabrück Polymerase-Kettenreaktion (PCR) Die Polymerase-Kettenreaktion (englisch Polymerase Chain Reaction, PCR) ist eine
1. Einleitung S. 1 1.1. Zelladhäsionsmoleküle S. 1 1.2. Die Immunglobulin-Superfamilie S. 2. 1.2.1. Das neurale Zelladhäsionsmolekül NCAM S.
 Inhaltsverzeichnis 1. Einleitung S. 1 1.1. Zelladhäsionsmoleküle S. 1 1.2. Die Immunglobulin-Superfamilie S. 2 1.2.1. Das neurale Zelladhäsionsmolekül NCAM S. 4 1.2.1.1. Molekulare Struktur von NCAM S.
Inhaltsverzeichnis 1. Einleitung S. 1 1.1. Zelladhäsionsmoleküle S. 1 1.2. Die Immunglobulin-Superfamilie S. 2 1.2.1. Das neurale Zelladhäsionsmolekül NCAM S. 4 1.2.1.1. Molekulare Struktur von NCAM S.
Zeitaufgelöste Fluoreszenzmessung zur Verwendung bei der Realtime-PCR
 Zeitaufgelöste Fluoreszenzmessung zur Verwendung bei der Realtime-PCR Nils Scharke, inano Abstract Die Verwendung neuartiger Seltenerd-Komplexe in Verbindung mit zeitaufgelöster Fluoreszenzmessung liefert
Zeitaufgelöste Fluoreszenzmessung zur Verwendung bei der Realtime-PCR Nils Scharke, inano Abstract Die Verwendung neuartiger Seltenerd-Komplexe in Verbindung mit zeitaufgelöster Fluoreszenzmessung liefert
Drosophila melanogaster
 Modul biol113 Zellbiologie Drosophila melanogaster Komponenten der angeborenen Immunabwehr Experimente 1) RT (Reverse Transkriptase)-PCR zum Nachweis einer AMP- Expression nach Infektion 1.1 PCR-Reaktion
Modul biol113 Zellbiologie Drosophila melanogaster Komponenten der angeborenen Immunabwehr Experimente 1) RT (Reverse Transkriptase)-PCR zum Nachweis einer AMP- Expression nach Infektion 1.1 PCR-Reaktion
Techniken der. Nukleinsäure- und. Protein-Biochemie
 Techniken der Nukleinsäure- und Protein-Biochemie Techniken der Nukleinsäure-Biochemie (Primer-) Synthese Restriktion, Analyse Ligation Expression PCR Klonierung in einen Expressions- Vektor Transformation
Techniken der Nukleinsäure- und Protein-Biochemie Techniken der Nukleinsäure-Biochemie (Primer-) Synthese Restriktion, Analyse Ligation Expression PCR Klonierung in einen Expressions- Vektor Transformation
Rekombinante Antikorperfragmente fur die. Zoonosediagnostik
 Rekombinante Antikorperfragmente fur die Zoonosediagnostik Von der Fakultat fur Lebenswissenschaften der Technischen Universitat Carolo-Wilhelmina zu Braunschweig zur Erlangung des Grades eines Doktors
Rekombinante Antikorperfragmente fur die Zoonosediagnostik Von der Fakultat fur Lebenswissenschaften der Technischen Universitat Carolo-Wilhelmina zu Braunschweig zur Erlangung des Grades eines Doktors
Vergleich transgene Pflanzen und traditionelle Züchtung
 Vergleich transgene Pflanzen und traditionelle Züchtung Transgene Pflanzen - Veränderung der genetisch bedingten Merkmale, z.b. größere Früchte, bleiben länger frisch - Ein gewünschtes Merkmal kann exakt
Vergleich transgene Pflanzen und traditionelle Züchtung Transgene Pflanzen - Veränderung der genetisch bedingten Merkmale, z.b. größere Früchte, bleiben länger frisch - Ein gewünschtes Merkmal kann exakt
Protokoll Versuch A1 Klonierung des Tyro3-D1D2-Fragments mittels PCR
 Protokoll Versuch A1 Klonierung des Tyro3-D1D2-Fragments mittels PCR Gruppe 8 Susanne Duncker und Friedrich Hahn Einleitung und Aufgabenstellung Ziel dieses Versuchs ist es, das Gen für ein bestimmtes
Protokoll Versuch A1 Klonierung des Tyro3-D1D2-Fragments mittels PCR Gruppe 8 Susanne Duncker und Friedrich Hahn Einleitung und Aufgabenstellung Ziel dieses Versuchs ist es, das Gen für ein bestimmtes
Genexpressionsregulation
 Genexpressionsregulation Genexpressionsregulation Different tissue types 1 2 3 4 5 6 7 8 Taken from Caron et al., 2001 Verschiedene Ebenen der Genexpressionsregulation Epigenetic mechanisms Transkriptionskontrolle
Genexpressionsregulation Genexpressionsregulation Different tissue types 1 2 3 4 5 6 7 8 Taken from Caron et al., 2001 Verschiedene Ebenen der Genexpressionsregulation Epigenetic mechanisms Transkriptionskontrolle
4.1. Herstellung des CH2/CH3-trunkierten dimerisierten anti-cd30-igg1-tnf- Fusionsproteins
 ERGEBNISSE 29 4. Ergebnisse 4.1. Herstellung des CH2/CH3-trunkierten dimerisierten anti-cd3-igg1-tnf- Fusionsproteins Im vorliegenden Immunzytokin wurden die Domänen CH2/CH3 des humanen Fc-Fragmentes durch
ERGEBNISSE 29 4. Ergebnisse 4.1. Herstellung des CH2/CH3-trunkierten dimerisierten anti-cd3-igg1-tnf- Fusionsproteins Im vorliegenden Immunzytokin wurden die Domänen CH2/CH3 des humanen Fc-Fragmentes durch
DNA versus RNA. RNA Instabilität
 DNA versus RNA DNA stellt den eigentlichen Speicher genetischer Information dar, während RNA als Informationsüberträger und katalytisch in der Proteinbiosynthese agiert. Warum dient DNA und nicht RNA als
DNA versus RNA DNA stellt den eigentlichen Speicher genetischer Information dar, während RNA als Informationsüberträger und katalytisch in der Proteinbiosynthese agiert. Warum dient DNA und nicht RNA als
Molekulare Mechanismen der Signaltransduktion. 06 - Kartierung des AXR1 Gens + early auxin-induced genes Folien: http://tinyurl.
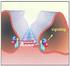 Molekulare Mechanismen der Signaltransduktion 06 - Kartierung des AXR1 Gens + early auxin-induced genes Folien: http://tinyurl.com/modul-mms bisheriges Modell auxin auxin AXR1 auxin response AXR1 potentieller
Molekulare Mechanismen der Signaltransduktion 06 - Kartierung des AXR1 Gens + early auxin-induced genes Folien: http://tinyurl.com/modul-mms bisheriges Modell auxin auxin AXR1 auxin response AXR1 potentieller
Dr. Peter Kainz Einführung in die Nucleinsäure-Biochemie Teil 2. III.Einführung in die Polymerase Chain Reaction (PCR)
 Dr. Peter Kainz Einführung in die Nucleinsäure-Biochemie Teil 2 III.Einführung in die Polymerase Chain Reaction (PCR) DI Praktikumsergebnisse SS 2009 Restriktionsverdau MI V MI N DI Praktikumsergebnisse
Dr. Peter Kainz Einführung in die Nucleinsäure-Biochemie Teil 2 III.Einführung in die Polymerase Chain Reaction (PCR) DI Praktikumsergebnisse SS 2009 Restriktionsverdau MI V MI N DI Praktikumsergebnisse
Platzhalter für Bild
 Instrumentelle Bioanalytik in der Molekularbiologie Anke Neumann Platzhalter für Bild KIT die Kooperation von Forschungszentrum Karlsruhe GmbH und Universität Karlsruhe (TH) www.kit.edu Motivation und
Instrumentelle Bioanalytik in der Molekularbiologie Anke Neumann Platzhalter für Bild KIT die Kooperation von Forschungszentrum Karlsruhe GmbH und Universität Karlsruhe (TH) www.kit.edu Motivation und
Gentechnik in Lebens- und Futtermitteln
 BfR - Jubiläum FEDERAL INSTITUTE FOR RISK ASSESSMENT Gentechnik in Lebens- und Futtermitteln Dr. Jutta Zagon Produktidentität, Rückverfolgbarkeit und Neuartige Lebensmittel Thielallee 88-92, 14195 Berlin
BfR - Jubiläum FEDERAL INSTITUTE FOR RISK ASSESSMENT Gentechnik in Lebens- und Futtermitteln Dr. Jutta Zagon Produktidentität, Rückverfolgbarkeit und Neuartige Lebensmittel Thielallee 88-92, 14195 Berlin
MOL.504 Analyse von DNA- und Proteinsequenzen
 MOL.504 Analyse von DNA- und Proteinsequenzen Inhaltsübersicht Molekulares Klonieren Vektoren und ihre Eigenschaften Programme für Vektorkarten und virtuelles Klonieren Protein-Expression mrna-eigenschaften
MOL.504 Analyse von DNA- und Proteinsequenzen Inhaltsübersicht Molekulares Klonieren Vektoren und ihre Eigenschaften Programme für Vektorkarten und virtuelles Klonieren Protein-Expression mrna-eigenschaften
Exkurs 4: Oligonucleotide als Antisense Wirkstoffe
 Exkurs 4: ligonucleotide als Antisense Wirkstoffe Pharmazeutische Biochemie Antisense Wirkstoffe am Markt Fomivirsen (INN) Handelsname Vitravene Einsatz: Lokale Behandlung von Zytomegalie-Virus Infektionen
Exkurs 4: ligonucleotide als Antisense Wirkstoffe Pharmazeutische Biochemie Antisense Wirkstoffe am Markt Fomivirsen (INN) Handelsname Vitravene Einsatz: Lokale Behandlung von Zytomegalie-Virus Infektionen
Sequenziertechnologien
 Sequenziertechnologien Folien teilweise von G. Thallinger übernommen 11 Entwicklung der Sequenziertechnologie First Generation 1977 Sanger Sequenzierung (GOLD Standard) Second Generation 2005 454 Sequencing
Sequenziertechnologien Folien teilweise von G. Thallinger übernommen 11 Entwicklung der Sequenziertechnologie First Generation 1977 Sanger Sequenzierung (GOLD Standard) Second Generation 2005 454 Sequencing
MOL.504 Analyse von DNA- und Proteinsequenzen
 MOL.504 Analyse von DNA- und Proteinsequenzen Vorbereitung: Start des Serial Cloners ( unter Laufwerk K: im Ordner Win_SerialCloner2-5 Programm direkt im Ordner starten) K:\Win_SerialCloner2-5 (oder 2-6
MOL.504 Analyse von DNA- und Proteinsequenzen Vorbereitung: Start des Serial Cloners ( unter Laufwerk K: im Ordner Win_SerialCloner2-5 Programm direkt im Ordner starten) K:\Win_SerialCloner2-5 (oder 2-6
Musterlösung - Übung 5 Vorlesung Bio-Engineering Sommersemester 2008
 Aufgabe 1: Prinzipieller Ablauf der Proteinbiosynthese a) Erklären Sie folgende Begriffe möglichst in Ihren eigenen Worten (1 kurzer Satz): Gen Nukleotid RNA-Polymerase Promotor Codon Anti-Codon Stop-Codon
Aufgabe 1: Prinzipieller Ablauf der Proteinbiosynthese a) Erklären Sie folgende Begriffe möglichst in Ihren eigenen Worten (1 kurzer Satz): Gen Nukleotid RNA-Polymerase Promotor Codon Anti-Codon Stop-Codon
Neue DNA Sequenzierungstechnologien im Überblick
 Neue DNA Sequenzierungstechnologien im Überblick Dr. Bernd Timmermann Next Generation Sequencing Core Facility Max Planck Institute for Molecular Genetics Berlin, Germany Max-Planck-Gesellschaft 80 Institute
Neue DNA Sequenzierungstechnologien im Überblick Dr. Bernd Timmermann Next Generation Sequencing Core Facility Max Planck Institute for Molecular Genetics Berlin, Germany Max-Planck-Gesellschaft 80 Institute
Life Science Konferenz 05. Mai 2010 in Jena. Chancen und Möglichkeiten - Real-time PCR
 Life Science Konferenz 05. Mai 2010 in Jena Chancen und Möglichkeiten - Real-time PCR Die 3 Phasen der PCR 1. Denaturierung DNA-Doppelstrang wird in Einzelstränge aufgeschmolzen Für 30 sec auf 95 C erhitzen
Life Science Konferenz 05. Mai 2010 in Jena Chancen und Möglichkeiten - Real-time PCR Die 3 Phasen der PCR 1. Denaturierung DNA-Doppelstrang wird in Einzelstränge aufgeschmolzen Für 30 sec auf 95 C erhitzen
Kapillarelektrophorese DNA-Sequenzierung
 Kapillarelektrophorese DNA-Sequenzierung DNA Kettenanalyse oder DNA-Sequenzierung wird bei der Anordnung der Primärstruktur und Bestimmung der Nukleotid-Basensequenz verwendet. Die Analyse basiert auf
Kapillarelektrophorese DNA-Sequenzierung DNA Kettenanalyse oder DNA-Sequenzierung wird bei der Anordnung der Primärstruktur und Bestimmung der Nukleotid-Basensequenz verwendet. Die Analyse basiert auf
Molekulare Verfahren im Kontext mit klinischer Praxis und Bestandsbetreuung beim Schwein
 Molekulare Verfahren im Kontext mit klinischer Praxis und Bestandsbetreuung beim Schwein DNA-Extraktion Photometrie Polymerase-Kettenreaktion (PCR) Restriktionsanalyse Agarose-Gelelektrophorese Polyacrylamid-Gelelektrophorese
Molekulare Verfahren im Kontext mit klinischer Praxis und Bestandsbetreuung beim Schwein DNA-Extraktion Photometrie Polymerase-Kettenreaktion (PCR) Restriktionsanalyse Agarose-Gelelektrophorese Polyacrylamid-Gelelektrophorese
Einführung in die Bioinformatik
 Einführung in die Bioinformatik Kay Nieselt SS 01 8. It s hip to chip - von Microarrays zu personalisierter Medizin WSI/ZBIT, Eberhard Karls Universität Tübingen Das menschliche Genom (~.000.000.000 Basenpaare)
Einführung in die Bioinformatik Kay Nieselt SS 01 8. It s hip to chip - von Microarrays zu personalisierter Medizin WSI/ZBIT, Eberhard Karls Universität Tübingen Das menschliche Genom (~.000.000.000 Basenpaare)
Praktikumsteil: 3 - RACE-PCR und Klonierung von MADS-Box- Genen aus Monokotylen
 Praktikumsteil: 3 - RACE-PCR und Klonierung von MADS-Box- Genen aus Monokotylen Vorbereitung auf diesen Praktikumsteil: Organisation - Für den Bioinformatik-Teil benötigen Sie pro Gruppe einen Laptop -
Praktikumsteil: 3 - RACE-PCR und Klonierung von MADS-Box- Genen aus Monokotylen Vorbereitung auf diesen Praktikumsteil: Organisation - Für den Bioinformatik-Teil benötigen Sie pro Gruppe einen Laptop -
Das zentrale Dogma der Molekularbiologie:
 Das zentrale Dogma der Molekularbiologie: DNA Transkription RNA Translation Protein 1 Begriffserklärungen GENOM: Ist die allgemeine Bezeichnung für die Gesamtheit aller Gene eines Organismus GEN: Ist ein
Das zentrale Dogma der Molekularbiologie: DNA Transkription RNA Translation Protein 1 Begriffserklärungen GENOM: Ist die allgemeine Bezeichnung für die Gesamtheit aller Gene eines Organismus GEN: Ist ein
Was sind MICROARRAYS? Microarrays sind Technologieplattformen zur Messung der Aktivität einer großen Anzahl von Genen.
 MICROARRAYS Was sind Microarrays? Welche Technologieplattformen gibt es? Beispiel: Rot-Grün Chip Wie wird ein Chip hergestellt (Film)? Welche Fragen kann man mit Chips beantworten? Datenfluß: Experiment-Design
MICROARRAYS Was sind Microarrays? Welche Technologieplattformen gibt es? Beispiel: Rot-Grün Chip Wie wird ein Chip hergestellt (Film)? Welche Fragen kann man mit Chips beantworten? Datenfluß: Experiment-Design
Gentransfer in höhere Eukaryonten
 63 Gentransfer in höhere Eukaryonten von Florian Rüker, Wien Mit Hilfe der Methoden der DNA-Rekombination ist es möglich geworden, eine Vielzahl von Genen zu isolieren und zu charakterisieren. Die funktionelle
63 Gentransfer in höhere Eukaryonten von Florian Rüker, Wien Mit Hilfe der Methoden der DNA-Rekombination ist es möglich geworden, eine Vielzahl von Genen zu isolieren und zu charakterisieren. Die funktionelle
