Inhalt. Was ist Bioinformatik? Was ist Genomik? Was ist Metagenomik? Metagenomische Analyse. Was ist Bioinformatik? Warum Bioinformatik?
|
|
|
- Silke Dresdner
- vor 7 Jahren
- Abrufe
Transkript
1 Metagenomik Daniel H. Huson Inhalt Was ist Bioinformatik? Was ist enomik? Was ist Metagenomik? Metagenomische nalyse Inhalt Was ist Bioinformatik? Was ist enomik? Was ist Metagenomik? Metagenomische nalyse orlesung rundlagen der Bioinformatik, SoSe Was ist Bioinformatik? Warum Bioinformatik? Was ist Bioinformatik? Warum Bioinformatik? Was ist Bioinformatik? 4 SOLID pplied Biosystems 5 Forschung Modelle, lgorithmen und Software zur Verarbeitung von biologischen Daten Lehre Interdisziplinäre usbildung in Bioinformatik, Informatik, Mathematik, Biologie und Chemie 6
2 Pacific Symposium on Biocomputing (PSB) 2009 Bioinformatik erman Conference on Bioinformatics 2009 Halle (Saale), September 28-30, 2009 WBI 2009 Workshop on lgorithms in Bioinformatics CSB 2009 workshop on Comparative enome nalyses of Bacterial enomes and pplications Inhalt Was ist Bioinformatik? Was ist enomik? Was ist Metagenomik? Metagenomische nalyse Charles Darwin und die Evolution by eorge Richmond Online Journal of Bioinformatics u.v.m. 7 8 Darwin: "species have changed, and are still slowly changing by the preservation and accumulation of successive slight favorable variations." 9 DNS Biomolekulare rundlage der Evolution DNS und Proteine 1869 Miescher entdeckt DNS in der Küche des Schlosses Hohentübingen Friedrich Miescher ( ) C C... Wiki.org 1953 Francis Crick, Rosalind Franklin, James Watson, und Maurice Wilkins - Struktur der DNS ist eine Doppelhelix - Reihenfolge der Basen bildet einen Kode, der durch die Zelle in ein Protein übersetzt wird 11 12
3 Protein Sequenzierung 1955 Biochemiker Frederick Sanger bestimmt die erste vollständige minosäurensequenz eines Proteins, Insulin. DNS Sequenzierung 1975 Frederick Sanger entwickelt die Kettenabbruchmethode zur Sequenzierung von DNS enomik Die enomik ist das Studium der enomsequenz einzelner Organismen enomgrößen: Bakterien: 1-10 Millionen Basen (Mb) Fruchtfliege: 140 Mb Mensch: 3 Milliarden Basen (b) Sequenzierung Sanger Sequenzierung Sanger Sequenzierung C CCCC C C C C C base pairs of DN (x150000) elesene DNS Sequenz Probe DNS Molekül Datenbank heißt Read DNS Polymerase XXXCCCCCCCXXX CCCCC C C C C C C C DNS Polymerase XXXCCCCCCCXX CCC C C C C C C C C C 16 Deoxynukleotide 17 Deoxynukleotide efärbte di-deoxynukleotide 18
4 Kapillar-echnologie Sequenzfabriken Kapillare Sanger Sequenzierung Eigenschaften: Readlänge ~800 bp C ~99.9% enauigkeit 96 Sequenzen parallel verarbeitet Sequenzierung & ssemblierung ssemblierung enomik 2001 Die Sequenzierung des menschlichen enoms Mondlandung Schrotschuss Klonierung und Zerteilung der DNS Sequenzierung ssemblierung und nnotation
5 enomik enomsequenzen von vielen Modellorganismen mittels Sanger bestimmt: Mensch, Maus, Hund, Ratte, Fruchtfliege, Hefe, cker- Schmalwand, Pappel, verschiedene Bakterien und Viren... Neue Sequenzierungstechnologien b 2005 neue Verfahren Sequenzierungsprojekte Erste neue Sequenziertechnik Emulsion-basierte mplifikation DNS Kugel in die PicoiterPlate M laden ) Jeder Kugel wird ein DNS Fragment zugeordnet Kugel in eine PicoiterPlate M laden Enzyme hinzufügen Zentrifugation Nature, 2005 Source: Stephan C. Schuster, Penn State C) Mikroreaktoren auflösen, mit DNS beladene Kugel selektieren B) Kugel und Reagenzien werden in Wasser-in-Öl Mikroreaktoren eingebracht 44 µm Source: Source:
6 Sequenzierung-mittels-Synthese Parallele Sequenzierung der Fragmente: Fluss Fluss CCCCC CC CC CCCC Sequenzierung-mittels-Synthese Parallele Sequenzierung der Fragmente: Fluss Fluss Fluss usw... CCCCC CC CC CCCC Sequenzierung-mittels-Synthese Basenbestimmung durch nalyse einer Serie von Bildern Source: C DNS Reads zufällig auf einem räger verteilt Solexa Sequenzierung Basenbestimmung durch Bildanalyse egenüberstellung der echnologien Readlänge Basen per Lauf Kosten per Base Sanger < kb > < Mb >10 Solexa <75 10 b 1 Sequenzierungsprojekte nzahl der abgeschlossenen oder zurzeit durchgeführten Projekte: ca Bakterien, ca. 100 rchaebakterien, ca. 100 Eukaryoten Werte ändern sich stetig und deshalb stimmen die ngaben nur größenordnungsmäßig 35 36
7 Sequenzierungsprojekte Inhalt Wie viele rten gibt es? 1000 enomes Projekt: Sequenzierung der enome von 1000 verschiedenen Menschen 1001 enomes Projekt: Sequenzierung von 1001 verschiedenen enomen von Pflanzen (rabidopsis thaliana) EB (enomic Encyclopedia of Bacteria and rchaea) Projekt: Sequenzierung von 100 Prokaryoten Was ist Bioinformatik? Was ist enomik? Was ist Metagenomik? Metagenomische nalyse Eine ungelöste Hauptfrage: nzahl der verschiedenen rten? Nicht mal bis auf einige rößenordnungen genau beantwortet Einige Schätzungen 3-50 Millionen rten von rthropoden Millionen rten von Fadenwürmern Once the diversity of the microbial world is catalogued, it will make astronomy look like a pitiful science Julian Davies, Professor Emeritus, Microbiology and Immunology, UBC 39 Identifizierte Moderne Spezies ~1.7 Million benannte rten Pflanzen, inkl.: Moose Farne 980 nacktsamige zweikeimblättrige einkeimblättrige Pilze Flechten Prokaryoten ~ iere, inkl.: wirbellose: Insekten Weichtiere Krustentiere andere Wirbeltiere: Fische mphibien Reptilien Vögel Säugetiere (Was ist eine Spezies?) Wikipedia listet mehr als 20 verschiedene Definitionen des Begriffes Spezies Metagenomik Das Studium der DNS von unkultivierten Organismen > 99% aller Mikroben nicht kultivierbar report.de Ein enom: esamtheit der genetischen Information eines einzelnen Organismus Ein Metagenom: esamtheit der genetischen Information einer ruppe von Organismen Quelle: Sequenzen für ~
8 ypische Quellen für Metagenome lobal Ocean Sampling Expedition (JCVI) Darm Mikrobiota Bodenproben Meeresproben Bohrkerne aus dem Meeresgrund Luftproben Uralte DNS soils.usda.gov Rusch et al. (2007): 41 Wasserproben röße gefiltert 0,1-0,8 µm Sanger Sequenzierung 7,7 Million Reads Readlänge ~822bp ~ 5,9 b Sequenz Niedriger nteil klonaler Organismen Mikroheterogenität Yooseph et al. (2007): 6 Million Proteine Lineare Entdeckungsrate urnbaugh et al (2006) Mikrobielle DNS aus ob/ob, ob/+, +/+ Mäusen Sanger Sequenzierung: 39.5 Mb Readlänge ~ 750 bp 454 Sequenzierung: 160 Mb Readlänge ~ 93 bp Obesität-assozierte Darm Mikrobiom Veränderung der Häufigkeit von Bacteroidetes und Firmicutes Veränderung der funktionalen Kapazität (in Richtung Energieaufnahme) Nature, Vol /28 December 2006 doi: /nature Mammut Projekt Metatranskriptomik einer Bodenprobe Inhalt DNS aus einem Mammut ( Jahre alt, Permafrost) DNS aus einem ram Knochen extrahiert 454 Sequenzierung Reads ~ Länge ~ 95 bp Urich et al (2008): RNS in cdns zurückgeschrieben 454 Sequenzierung: Reads: ~ Länge: ~ 98 bp RNS ypen: ~ 75% rrns Reads ~ 8% mrns Reads ~ 17% andere rrns nalyse Was ist Bioinformatik? Was ist enomik? Was ist Metagenomik? Metagenomische nalyse 46 mrns nalyse 47 48
9 Zwei Hauptfragen für die Bioinformatik Zwei Hauptfragen für die Bioinformatik Wer ist da? axonomische nalyse Wer ist da draußen? Welche Organismen? In welchen Mengen? Was machen sie? Welche ene vorhanden? ktive Stoffwechselwege? In welchen Mengen? Wer ist da draußen? Welche Organismen? In welchen Mengen? Was machen sie? Welche ene vorhanden? ktive Stoffwechselwege? In welchen Mengen? Hauptprinzip: Ähnlichkeitssuche Für jedes sequenziertes Read: Finde ähnliche Referenzsequenzen in einer Datenbank bekannter Spezies Benutze sie um das Read in die axonomie des Lebens zu plazieren rundlage für biologische Fragen, z.b.: Wie funktioniert eine emeinschaft von Mikroben? rundlage für biologische Fragen, z.b.: Wie funktioniert eine emeinschaft von Mikroben? Wie evolvieren Mikroben? 49 Wie evolvieren Mikroben? Metagenom nalyse Sequenzvergleich mit BLS Die NCBI-NR Datenbank Verarbeitungs pipeline Probe Metagenom DNS Reads Sequenz Vergleich nr nt env-nr env-nt Vergleichsdaten Interaktive nalyse und Visualisierung Das Programm BLS vergleicht Reads gegen eine Datenbank und meldet ähnliche Sequenzen >gi ref ZP_ flagellar motor switch protein [Campylobacter lari RM2100] Score = 33.9 bits (76), Expect = 1.8 Identities = 13/26 (50%), Positives = 19/26 (73%) Query: 79 LMFVFDDLVEENIREIINRDKK 2 LMF FDD++ + N IRE++ DK+ Sbjct: 243 LMFFDDISQLSNIREVLKDKR 268 NCBI-NR ist die größte Proteindatenbank der Welt Mehr als 50 Millionen Einträge Über die Hälfte Homo sapiens Mehr als 1,2 Milliarden minosäuren (NR= nicht redundant) enome Referenz Datenbanken 52 BLS - das meistbenutzte ool der Bioinformatik Original BLS (1990) mal zitiert apped BLS (1997) mal zitiert 53 nr nt enome env-nr env-nt 54
10 Die NCBI-N Datenbank Weitere Datenbanken Metagenom nalyse NCBI-N enthält DNS Sequenzen Mehr als 3 Millionen Einträge Ca 10% Homo sapiens Mehr als 16 Milliarden Nukleotide Environmental-NR Proteinsequenzen aus Metagenomik Proben Environmental-N DNS Sequenzen aus Metagenomik Proben enomdatenbanken Hunderte von rten Probe Metagenom DNS Reads Sequenz Vergleich nr nt env-nr env-nt Vergleichsdaten Interaktive nalyse und Visualisierung nr nt env-nr env-nt nr nt env-nr env-nt enome Referenz Datenbanken enome enome Identifizierung durch Vergleich Einsortierung der Reads in die axonomie nalyse mittels axonomie der rten DNS Read Ein Read hat oft Ähnlichkeit zu mehreren Referenzsequenzen: Einsortierung der Reads in die axonomie: Probe CCCC...C >gi ref ZP_ flagellar motor switch proteinfli [Campylobacter lari RM2100] Score = 33.9 bits (76), Expect = 1.8 Identities = 13/26 (50%), Positives = 19/26 (73%) BLS reffer Query: 79 LMFVFDDLVEENIREIINRDKK 2 LMF FDD++ + N IRE++ DK+ Sbjct: 243 LMFFDDISQLSNIREVLKDKR 268 >gi ref ZP_ flagellar motor switch protein [Campylobacter lari RM2100] Score = 33.9 bits (76), Expect = 1.8 Identities = 13/26 (50%), Positives = 19/26 (73%) Ordnung >gi gb P flagellar motor switch protein Fli [Helicobacter hepaticus CC 51449] Score = 33.5 bits (75), Expect = 2.4 Identities = 13/26 (50%), Positives = 20/26 (76%) Query: 79 LMFVFDDLVEENIREIINRDKK 2 +MF F+D++ ++ N IREI+ DKK Sbjct: 244 MMFFEDISKLDNNIREILKIDKK 269 Query: 79 LMFVFDDLVEENIREIINRDKK 2 LMF FDD++ + N IRE++ DK+ Sbjct: 243 LMFFDDISQLSNIREVLKDKR 268 >gi emb CE FLELLR MOOR SWICH PROEIN FLI [Wolinella succinogenes] Score = 32.7 bits (73), Expect = 4.1 Identities = 13/26 (50%), Positives = 19/26 (73%) Zuordnung des Reads Campylobacter lari RM Query: 79 LMFVFDDLVEENIREIINRDKK 2 +MF F+D+ ++ N IREI+ DKK Sbjct: 242 MMFFEDIEKLDNNIREILKVDKK 267 Neue, unbekannte rt Regelfall: Metagenom enthält viele unbekannte rten 59 60
11 axonomie des Lebens Beispiel: Darmflora einer Maus Vergleichende nalyse Klassifizierung der bekannten rten ~285,000 axa Hauptebenen: 25,000 Prokaryoten Königreich 84,000 iere Stamm 65,000 Pflanzen Klasse 17,000 Viren Ordnung Familie attung rt Lactobacillus: eil der Darmflora, verarbeitet Lactose 62 Veschiebung der nteile dieser beiden Phyla 63 Zwei Hauptfragen für die Bioinformatik ene Ontology Beispiel O Prozesse Wer ist da draußen? Welche Organismen? In welchen Mengen? Was machen sie? Welche ene vorhanden? ktive Stoffwechselwege? In welchen Mengen? rundlage für biologische Fragen, z.b.: Wie funktioniert eine emeinschaft von Mikroben? Wie evolvieren Mikroben? 64 Die ene Ontology stellt ein Vokabular bereit, um ene zu beschreiben Drei Ontologien: Function Funktion des enes Process n welchen Prozessen beteiligt? Component In welchem eil der Zelle? Ca Begriffe 65 66
12 Beispiel O Funktion Beispiel O Zellteil Was machen sie? Funktionale nalyse Hauptprinzip: Ähnlichkeitssuche Für jedes sequenziertes Read: Finde ähnliche Referenzsequenzen in einer Datenbank bekannter Spezies Benutze sie um das Read in die O Ontologie zu plazieren Metagenom nalyse Funktionale nalyse BLS O Ontologien reffer Funktion Prozess eil Prozess Einordung eines Reads in O Process Probe Metagenom DNS Reads Sequenz Vergleich nr nt env-nr env-nt Vergleichsdaten Interaktive nalyse und Visualisierung Read M 1 M 2 M 3 M 4 protein binding response to stress signal transduction cell communication nucleus cellular process enome Referenz Datenbanken M 5 cell part cytosol cell communication 70 Einordunung??? 71? response to stress signal transduction 72
13 Beispiel: Darmflora einer Maus Vergleichende nalyse Vergleichende nalyse 73 Obese Maus: Signifikant mehr ene zur Energieextrahierung 74 Obese Maus: Signifikant mehr ene zur Energieextrahierung Nature, Vol /28 December 2006 doi: /nature usblick Ende der technologischen Fortschritte in der Biologie nicht in Sicht Umwelt enthält sehr viele bisher unbekannte Organismen Bioinformatik hilft, die zwei rundfragen zu beantworten: Who is out there? What are they doing? 76
Von der DNA zur Datenbank: Sequenzierung & Assemblierung
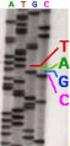 Vorlesung Einführung in die Bioinforma4k SoSe 2012 Von der DN zur Datenbank: Sequenzierung & ssemblierung Prof. Daniel Huson ZBI enter for Bioinformatics Entdeckung der DN Friedrich Miescher (1844-1895)
Vorlesung Einführung in die Bioinforma4k SoSe 2012 Von der DN zur Datenbank: Sequenzierung & ssemblierung Prof. Daniel Huson ZBI enter for Bioinformatics Entdeckung der DN Friedrich Miescher (1844-1895)
A T C G G C T A A T A T
 Vorlesung*Einführung*in*die*Bioinforma4k*SoSe*2013* * Von*der*DNA*zur*Datenbank:* Sequenzierung*&*Assemblierung* * Prof.&Daniel&Huson& ZBIT Center for Bioinformatics Singapore Center on Environmental Life
Vorlesung*Einführung*in*die*Bioinforma4k*SoSe*2013* * Von*der*DNA*zur*Datenbank:* Sequenzierung*&*Assemblierung* * Prof.&Daniel&Huson& ZBIT Center for Bioinformatics Singapore Center on Environmental Life
1. Die Gene befinden sich im Zellkern. Zellleib. 2. Chromosomen bestehen aus DNA. 4. Ein Gen ist ein DNA-Abschnitt 7. Protein-Herstellung nach Bedarf
 rundlagen 1. Die ene befinden sich im Zellkern 3. lle hromosomen zusammen bilden das enom Zellleib Bakterium Pflanzenzelle menschliches enom Zellkern Muskelzelle Nervenzelle DN 2. hromosomen bestehen aus
rundlagen 1. Die ene befinden sich im Zellkern 3. lle hromosomen zusammen bilden das enom Zellleib Bakterium Pflanzenzelle menschliches enom Zellkern Muskelzelle Nervenzelle DN 2. hromosomen bestehen aus
Bioinformatik II: Phylogenetik
 Bioinformatik II: Phylogenetik phylogenetisch Phylai: griechische Klans phylum: der Stamm phylogenetisch: die Stammesgeschichte von Lebewesen betreffend Hierarchien der Klassifikation: Domäne: Eukaryonten
Bioinformatik II: Phylogenetik phylogenetisch Phylai: griechische Klans phylum: der Stamm phylogenetisch: die Stammesgeschichte von Lebewesen betreffend Hierarchien der Klassifikation: Domäne: Eukaryonten
Synthetische Biologie
 Synthetische Biologie Segen oder Fluch? http://www.kwick.de Science Bridge - SG 19.11.2010 1 Gliederung 2 Was ist Synthetische Biologie? Fortschritt und Potential der synthetischen Biologie Ethische Aspekte
Synthetische Biologie Segen oder Fluch? http://www.kwick.de Science Bridge - SG 19.11.2010 1 Gliederung 2 Was ist Synthetische Biologie? Fortschritt und Potential der synthetischen Biologie Ethische Aspekte
Attached! Proseminar Netzwerkanalyse SS 2004 Thema: Biologie
 Rheinisch-Westfälischen Technischen Hochschule Aachen Lehr- und Forschungsgebiet Theoretische Informatik Prof. Rossmanith Attached! Proseminar Netzwerkanalyse SS 2004 Thema: Biologie Deniz Özmen Emmanuel
Rheinisch-Westfälischen Technischen Hochschule Aachen Lehr- und Forschungsgebiet Theoretische Informatik Prof. Rossmanith Attached! Proseminar Netzwerkanalyse SS 2004 Thema: Biologie Deniz Özmen Emmanuel
Molekularbiologische Datenbanken
 Molekularbiologische Datenbanken Übungen Sommersemester 2004 Silke Trißl Prof. Ulf Leser Wissensmanagement in der Bioinformatik Organisatorisches Mittwoch 11 13 Uhr, RUD26 0'313 Mi, 05. Mai 2004 entfällt
Molekularbiologische Datenbanken Übungen Sommersemester 2004 Silke Trißl Prof. Ulf Leser Wissensmanagement in der Bioinformatik Organisatorisches Mittwoch 11 13 Uhr, RUD26 0'313 Mi, 05. Mai 2004 entfällt
Neue DNA Sequenzierungstechnologien im Überblick
 Neue DNA Sequenzierungstechnologien im Überblick Dr. Bernd Timmermann Next Generation Sequencing Core Facility Max Planck Institute for Molecular Genetics Berlin, Germany Max-Planck-Gesellschaft 80 Institute
Neue DNA Sequenzierungstechnologien im Überblick Dr. Bernd Timmermann Next Generation Sequencing Core Facility Max Planck Institute for Molecular Genetics Berlin, Germany Max-Planck-Gesellschaft 80 Institute
Wissenschaftlich-technische Entwicklungen im Bereich der Multiplex- und High-Throughput-Diagnostik. Karl J. Lackner
 Wissenschaftlich-technische Entwicklungen im Bereich der Multiplex- und High-Throughput-Diagnostik Karl J. Lackner Hochdurchsatzverfahren in der molekularen bzw. genetischen Diagnostik Next Generation-Sequenzierung
Wissenschaftlich-technische Entwicklungen im Bereich der Multiplex- und High-Throughput-Diagnostik Karl J. Lackner Hochdurchsatzverfahren in der molekularen bzw. genetischen Diagnostik Next Generation-Sequenzierung
Bioinformatik an der FH Bingen
 Bioinformatik an der FH Bingen Prof. Dr. Antje Krause 05.11.2010 Wie alles begann... 1955 erste Proteinsequenz (nach 12 Jahren Arbeit) veröffentlicht (Insulin vom Rind) Frederick Sanger MALWTRLRPLLALLALWPPPPA
Bioinformatik an der FH Bingen Prof. Dr. Antje Krause 05.11.2010 Wie alles begann... 1955 erste Proteinsequenz (nach 12 Jahren Arbeit) veröffentlicht (Insulin vom Rind) Frederick Sanger MALWTRLRPLLALLALWPPPPA
Gentechnologie für Einsteiger
 T. A. Brown Gentechnologie für Einsteiger 3. Auflage Aus dem Englischen übersetzt von Sebastian Vogel Spektrum Akademischer Verlag Heidelberg Berlin Vorwort Vorwort zur dritten englischen Auflage Vorwort
T. A. Brown Gentechnologie für Einsteiger 3. Auflage Aus dem Englischen übersetzt von Sebastian Vogel Spektrum Akademischer Verlag Heidelberg Berlin Vorwort Vorwort zur dritten englischen Auflage Vorwort
Vorlesungsthemen Mikrobiologie
 Vorlesungsthemen Mikrobiologie 1. Einführung in die Mikrobiologie B. Bukau 2. Zellaufbau von Prokaryoten B. Bukau 3. Bakterielles Wachstum und Differenzierung B. Bukau 4. Bakterielle Genetik und Evolution
Vorlesungsthemen Mikrobiologie 1. Einführung in die Mikrobiologie B. Bukau 2. Zellaufbau von Prokaryoten B. Bukau 3. Bakterielles Wachstum und Differenzierung B. Bukau 4. Bakterielle Genetik und Evolution
Sequenziertechnologien
 Sequenziertechnologien Folien teilweise von G. Thallinger übernommen 11 Entwicklung der Sequenziertechnologie First Generation 1977 Sanger Sequenzierung (GOLD Standard) Second Generation 2005 454 Sequencing
Sequenziertechnologien Folien teilweise von G. Thallinger übernommen 11 Entwicklung der Sequenziertechnologie First Generation 1977 Sanger Sequenzierung (GOLD Standard) Second Generation 2005 454 Sequencing
Bioinformatik: The Next Generation
 Bioinformatik: The Next Generation Prof. Dr. Caroline Friedel Lehr- und Forschungseinheit Bioinformatik Was ist Bioinformatik? Prof. Dr. Caroline Friedel, Tag der offenen Tür der LMU 2 Was ist Bioinformatik?
Bioinformatik: The Next Generation Prof. Dr. Caroline Friedel Lehr- und Forschungseinheit Bioinformatik Was ist Bioinformatik? Prof. Dr. Caroline Friedel, Tag der offenen Tür der LMU 2 Was ist Bioinformatik?
Antwort: 2.Uracil. Antwort: 2. durch Wasserstoffverbindungen. Adenin, Cystein und Guanin kommen alle in der RNA und DNA vor.
 Antwort: 2.Uracil Adenin, Cystein und Guanin kommen alle in der RNA und DNA vor. Thymin kommt nur in der DNA vor; Uracil nimmt seinen Platz in den RNA- Molekülen ein. Antwort: 2. durch Wasserstoffverbindungen
Antwort: 2.Uracil Adenin, Cystein und Guanin kommen alle in der RNA und DNA vor. Thymin kommt nur in der DNA vor; Uracil nimmt seinen Platz in den RNA- Molekülen ein. Antwort: 2. durch Wasserstoffverbindungen
DNA: Aufbau, Struktur und Replikation
 DNA: Aufbau, Struktur und Replikation Biochemie Die DNA als Träger der Erbinformation Im Genom sind sämtliche Informationen in Form von DNA gespeichert. Die Information des Genoms ist statisch, d. h. in
DNA: Aufbau, Struktur und Replikation Biochemie Die DNA als Träger der Erbinformation Im Genom sind sämtliche Informationen in Form von DNA gespeichert. Die Information des Genoms ist statisch, d. h. in
Das internationale Human-Genom Projekt. Stand Ergebnisse Perspektiven
 Das internationale Human-Genom Projekt Stand Ergebnisse Perspektiven 2003 1953 April, 25 th, 1953 Watson, J.D., and F.H.C.Crick. 1953. Molecular Structure of Nucleic Acids: A Structure for Deoxynucleic
Das internationale Human-Genom Projekt Stand Ergebnisse Perspektiven 2003 1953 April, 25 th, 1953 Watson, J.D., and F.H.C.Crick. 1953. Molecular Structure of Nucleic Acids: A Structure for Deoxynucleic
In den Proteinen der Lebewesen treten in der Regel 20 verschiedene Aminosäuren auf. Deren Reihenfolge muss in der Nucleotidsequenz der mrna und damit
 In den Proteinen der Lebewesen treten in der Regel 20 verschiedene Aminosäuren auf. Deren Reihenfolge muss in der Nucleotidsequenz der mrna und damit in der Nucleotidsequenz der DNA verschlüsselt (codiert)
In den Proteinen der Lebewesen treten in der Regel 20 verschiedene Aminosäuren auf. Deren Reihenfolge muss in der Nucleotidsequenz der mrna und damit in der Nucleotidsequenz der DNA verschlüsselt (codiert)
Bioinformatik: The Next Generation
 Bioinformatik: The Next Generation Prof. Dr. Caroline Friedel Lehr- und Forschungseinheit Bioinformatik Was ist Bioinformatik? Theoretische und Praktische Informatik Statistik, Mathematik Molekularbiologie,
Bioinformatik: The Next Generation Prof. Dr. Caroline Friedel Lehr- und Forschungseinheit Bioinformatik Was ist Bioinformatik? Theoretische und Praktische Informatik Statistik, Mathematik Molekularbiologie,
Darwins Erben - Phylogenie und Bäume
 Vorlesung Einführung in die Bioinforma4k SoSe2011 Darwins Erben - Phylogenie und Bäume Prof. Daniel Huson ZBIT Center for Bioinformatics Center for Bioinformatics Charles Darwin und Bäume Darwin's Notizbuch
Vorlesung Einführung in die Bioinforma4k SoSe2011 Darwins Erben - Phylogenie und Bäume Prof. Daniel Huson ZBIT Center for Bioinformatics Center for Bioinformatics Charles Darwin und Bäume Darwin's Notizbuch
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr
 Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
[Grundlagen der] Physiologie der [Mikro-]organismen
![[Grundlagen der] Physiologie der [Mikro-]organismen [Grundlagen der] Physiologie der [Mikro-]organismen](/thumbs/54/33395711.jpg) [Grundlagen der] Physiologie der [Mikro-]organismen Heribert Cypionka Folien: www.icbm.de/pmbio... Teaching... Was ist Physiologie? Vgl. Morphologie, Taxonomie... Themen der Vorlesung: Gundlegende physiologische
[Grundlagen der] Physiologie der [Mikro-]organismen Heribert Cypionka Folien: www.icbm.de/pmbio... Teaching... Was ist Physiologie? Vgl. Morphologie, Taxonomie... Themen der Vorlesung: Gundlegende physiologische
Biologische Evolution. Prof. Dr. rer. nat. Wolfgang Schumann Institut für Genetik Universität Bayreuth
 Biologische Evolution Prof. Dr. rer. nat. Wolfgang Schumann Institut für Genetik Universität Bayreuth 1 Verwendete Quellen 1. Ulrich Kutschera: Evolutionsbiologie 2. GEOkompakt, Nr. 23: Evolution 3. Internet:
Biologische Evolution Prof. Dr. rer. nat. Wolfgang Schumann Institut für Genetik Universität Bayreuth 1 Verwendete Quellen 1. Ulrich Kutschera: Evolutionsbiologie 2. GEOkompakt, Nr. 23: Evolution 3. Internet:
Vertiefendes Seminar zur Vorlesung Biochemie I
 Vertiefendes Seminar zur Vorlesung Biochemie I 30.01.2015 Klausurvorbereitung: Gerhild van Echten-Deckert Rekombinante DNA Fon. +49-228-732703 Homepage: http://www.limes.uni-bonn.de Klärung einiger Begriffe:
Vertiefendes Seminar zur Vorlesung Biochemie I 30.01.2015 Klausurvorbereitung: Gerhild van Echten-Deckert Rekombinante DNA Fon. +49-228-732703 Homepage: http://www.limes.uni-bonn.de Klärung einiger Begriffe:
Bioinformatik: Schnittstelle zwischen Informatik und Life-Science
 Bioinformatik: Schnittstelle zwischen Informatik und Life-Science Andreas Zendler (PD Dr.rer.nat.Dr.phil.) GI / GChACM 12. ovember 2001 Inhaltsübersicht I. Einführung II. Bioinformatik III. Industrial
Bioinformatik: Schnittstelle zwischen Informatik und Life-Science Andreas Zendler (PD Dr.rer.nat.Dr.phil.) GI / GChACM 12. ovember 2001 Inhaltsübersicht I. Einführung II. Bioinformatik III. Industrial
Was ist der Promotor? Antwort: Eine spezielle Nucleotidsequenz auf der DNA, an der die RNA-Polymerase bindet um die Transkription zu starten.
 Was ist der Promotor? Antwort: Eine spezielle Nucleotidsequenz auf der DNA, an der die RNA-Polymerase bindet um die Transkription zu starten. Wie bezeichnet man den Strang der DNA- Doppelhelix, der die
Was ist der Promotor? Antwort: Eine spezielle Nucleotidsequenz auf der DNA, an der die RNA-Polymerase bindet um die Transkription zu starten. Wie bezeichnet man den Strang der DNA- Doppelhelix, der die
Bioinformatik. Margarethe Kyral
 Bioinformatik Margarethe Kyral Beispiel 1 neuer Krankheitserreger DNA-Sequenzierung Beispiel 1 neuer Krankheitserreger DNA-Sequenzierungsgeräte und -verfahren Beispiel 1 neuer Krankheitserreger Borreliose-Bakterium
Bioinformatik Margarethe Kyral Beispiel 1 neuer Krankheitserreger DNA-Sequenzierung Beispiel 1 neuer Krankheitserreger DNA-Sequenzierungsgeräte und -verfahren Beispiel 1 neuer Krankheitserreger Borreliose-Bakterium
Biologie:= Aber: Was ist eigentlich Leben?
 Biologie:= Lebenskunde Aber: Was ist eigentlich Leben? Prolog: Was ist Leben? Aktuelle Fragen: Sind wir Gott? Synthetische Biologie: Zusammenbau biologischer Systeme aus Molekülen. Kann man die Moleküle
Biologie:= Lebenskunde Aber: Was ist eigentlich Leben? Prolog: Was ist Leben? Aktuelle Fragen: Sind wir Gott? Synthetische Biologie: Zusammenbau biologischer Systeme aus Molekülen. Kann man die Moleküle
Informationstechnologie in der Pflanzenzüchtung. Biocomputing in einem Züchtungsunternehmen. Andreas Menze KWS SAAT AG, Einbeck
 Informationstechnologie in der Pflanzenzüchtung Biocomputing in einem Züchtungsunternehmen Andreas Menze KWS SAAT AG, Einbeck Biocomputing in einem Züchtungsunternehmen Biocomputing Was ist das? Wozu wird
Informationstechnologie in der Pflanzenzüchtung Biocomputing in einem Züchtungsunternehmen Andreas Menze KWS SAAT AG, Einbeck Biocomputing in einem Züchtungsunternehmen Biocomputing Was ist das? Wozu wird
Masterarbeit. Variantentolerantes Readmapping durch Locality Sensitive Hashing. Jens Quedenfeld November Gutachter: Sven Rahmann Dominik Köppl
 Masterarbeit Variantentolerantes Readmapping durch Locality Sensitive Hashing Jens Quedenfeld November 2015 Gutachter: Sven Rahmann Dominik Köppl Technische Universität Dortmund Fakultät für Informatik
Masterarbeit Variantentolerantes Readmapping durch Locality Sensitive Hashing Jens Quedenfeld November 2015 Gutachter: Sven Rahmann Dominik Köppl Technische Universität Dortmund Fakultät für Informatik
27 Funktionelle Genomanalysen Sachverzeichnis
 Inhaltsverzeichnis 27 Funktionelle Genomanalysen... 543 27.1 Einleitung... 543 27.2 RNA-Interferenz: sirna/shrna-screens 543 Gunter Meister 27.3 Knock-out-Technologie: homologe Rekombination im Genom der
Inhaltsverzeichnis 27 Funktionelle Genomanalysen... 543 27.1 Einleitung... 543 27.2 RNA-Interferenz: sirna/shrna-screens 543 Gunter Meister 27.3 Knock-out-Technologie: homologe Rekombination im Genom der
Gleichheit, Ähnlichkeit, Homologie
 Gleichheit, Ähnlichkeit, Homologie Identität (identity) Verhältnis der Anzahl identischer Aminosäuren zur Gesamtzahl der Aminosäuren; objektiv Ähnlichkeit (similarity) Verhältnis ähnlicher Aminosäuren
Gleichheit, Ähnlichkeit, Homologie Identität (identity) Verhältnis der Anzahl identischer Aminosäuren zur Gesamtzahl der Aminosäuren; objektiv Ähnlichkeit (similarity) Verhältnis ähnlicher Aminosäuren
Molekularbiologische Methoden
 Molekularbiologische Methoden im Lebensmittel-Labor Dr. rer. nat. Armin Pahl LADR GmbH MVZ Dr. Kramer & Kollegen 04152 803-0 www.ladr.de DNA 1866 Gregor Mendel veröffentlicht seine Versuche über Pflanzen-Hybriden,
Molekularbiologische Methoden im Lebensmittel-Labor Dr. rer. nat. Armin Pahl LADR GmbH MVZ Dr. Kramer & Kollegen 04152 803-0 www.ladr.de DNA 1866 Gregor Mendel veröffentlicht seine Versuche über Pflanzen-Hybriden,
Evolution & Genetik (Beispiel Hämoglobin) Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de
 Evolution & Genetik (Beispiel Hämoglobin) Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de DNA (Desoxyribonukleinsäure) 5 3 CGATGTACATCG GCTACATGTAGC 3 5 Doppelhelix Basen: Adenin,
Evolution & Genetik (Beispiel Hämoglobin) Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de DNA (Desoxyribonukleinsäure) 5 3 CGATGTACATCG GCTACATGTAGC 3 5 Doppelhelix Basen: Adenin,
Einblicke in das menschliche Erbgut (Genom) am Computer
 Einblicke in das menschliche Erbgut (Genom) am Computer Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de Binger Nacht der Wissenschaft - 16.04.2010 Das menschliche Genom ist entschlüsselt
Einblicke in das menschliche Erbgut (Genom) am Computer Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de Binger Nacht der Wissenschaft - 16.04.2010 Das menschliche Genom ist entschlüsselt
Algorithmische Bioinformatik
 lgorithmische Bioinformatik Stringalignment Ulf Leser Wissensmanagement in der Bioinformatik Inhalt dieser Vorlesung pproximative Stringvergleiche Dotplots Edit-bstand und lignment Naiver lgorithmus Ulf
lgorithmische Bioinformatik Stringalignment Ulf Leser Wissensmanagement in der Bioinformatik Inhalt dieser Vorlesung pproximative Stringvergleiche Dotplots Edit-bstand und lignment Naiver lgorithmus Ulf
V4 Analyse von Genomsequenzen
 V4 nalyse von enomsequenzen - ene identifizieren Intrinsische und Extrinsische Verfahren: Homologie bzw. Hidden Markov Modelle - ranskriptionsfaktorbindestellen identifizieren Position Specific Scoring
V4 nalyse von enomsequenzen - ene identifizieren Intrinsische und Extrinsische Verfahren: Homologie bzw. Hidden Markov Modelle - ranskriptionsfaktorbindestellen identifizieren Position Specific Scoring
DNA-Replikation. Konrad Beyreuther. Stefan Kins
 DNA-Replikation Konrad Beyreuther Stefan Kins DNA-Replikation Originalgetreue Verdopplung des genetischen Materials als Voraussetzung für die kontinuierliche Weitergabe der in der DNA verschlüsselten Information
DNA-Replikation Konrad Beyreuther Stefan Kins DNA-Replikation Originalgetreue Verdopplung des genetischen Materials als Voraussetzung für die kontinuierliche Weitergabe der in der DNA verschlüsselten Information
Primärstruktur. Wintersemester 2011/12. Peter Güntert
 Primärstruktur Wintersemester 2011/12 Peter Güntert Primärstruktur Beziehung Sequenz Struktur Proteinsequenzen, Sequenzdatenbanken Sequenzvergleich (sequence alignment) Sequenzidentität, Sequenzhomologie
Primärstruktur Wintersemester 2011/12 Peter Güntert Primärstruktur Beziehung Sequenz Struktur Proteinsequenzen, Sequenzdatenbanken Sequenzvergleich (sequence alignment) Sequenzidentität, Sequenzhomologie
V4 Analyse von Genomsequenzen
 V4 nalyse von enomsequenzen - ene identifizieren Intrinsische und Extrinsische Verfahren: Homologie bzw. Hidden Markov Modelle - ranskriptionsfaktorbindestellen identifizieren Position Specific Scoring
V4 nalyse von enomsequenzen - ene identifizieren Intrinsische und Extrinsische Verfahren: Homologie bzw. Hidden Markov Modelle - ranskriptionsfaktorbindestellen identifizieren Position Specific Scoring
fi Mikrobiologie > Teaching Vorlesung Allgemeine Biologie 21., 23., : Heribert Cypionka
 Vorlesung Allgemeine Biologie fi Mikrobiologie 21., 23., 29.11.: Heribert Cypionka 30.11.: Meinhard Simon Institut für Chemie und Biologie des Meeres Anreicherungskultur aus dem Watt vor Borkum weitere
Vorlesung Allgemeine Biologie fi Mikrobiologie 21., 23., 29.11.: Heribert Cypionka 30.11.: Meinhard Simon Institut für Chemie und Biologie des Meeres Anreicherungskultur aus dem Watt vor Borkum weitere
VORTRÄGE N447. Nordrhein-Westfälische Akademie der Wissenschaften WALTER SCHAFFNER OTTO SPANIOL. Wie werden unsere Gene ein- und ausgeschaltet?
 Nordrhein-Westfälische Akademie der Wissenschaften VORTRÄGE N447 WALTER SCHAFFNER Wie werden unsere Gene ein- und ausgeschaltet? OTTO SPANIOL Mobilfunk und Sicherheit - (Wie) Passt das zusammen? Westdeutscher
Nordrhein-Westfälische Akademie der Wissenschaften VORTRÄGE N447 WALTER SCHAFFNER Wie werden unsere Gene ein- und ausgeschaltet? OTTO SPANIOL Mobilfunk und Sicherheit - (Wie) Passt das zusammen? Westdeutscher
Aufgabe 1. Bakterien als Untersuchungsgegenstand!
 Genetik I Aufgabe 1. Bakterien als Untersuchungsgegenstand 1. Beschriften Sie die Abbildung zu den Bakterien. 2. Nennen Sie Vorteile, die Bakterien wie Escherichia coli so wertvoll für die genetische Forschung
Genetik I Aufgabe 1. Bakterien als Untersuchungsgegenstand 1. Beschriften Sie die Abbildung zu den Bakterien. 2. Nennen Sie Vorteile, die Bakterien wie Escherichia coli so wertvoll für die genetische Forschung
Brock Mikrobiologie kompakt (Pearson Studium - Biologie) 2015
 Michael T. Madigan, John M. Martinko, David A. Stahl, David P. Clark Brock Mikrobiologie kompakt (Pearson Studium - Biologie) 2015 Taschenbuch: 720 Seiten Verlag: Pearson Studium; Auflage: 13 (1. Januar
Michael T. Madigan, John M. Martinko, David A. Stahl, David P. Clark Brock Mikrobiologie kompakt (Pearson Studium - Biologie) 2015 Taschenbuch: 720 Seiten Verlag: Pearson Studium; Auflage: 13 (1. Januar
Bioinformatik I: Grundlagen der Gentechnik
 Bioinformatik I: Grundlagen der Gentechnik Dr. Maik Böhmer Institut für Biologie und Biotechnologie der Pflanzen Schlossplatz 7 Schwerpunkte: Vorlesung 1: Einführung & Enzyme der Gentechnik Vorlesung 2:
Bioinformatik I: Grundlagen der Gentechnik Dr. Maik Böhmer Institut für Biologie und Biotechnologie der Pflanzen Schlossplatz 7 Schwerpunkte: Vorlesung 1: Einführung & Enzyme der Gentechnik Vorlesung 2:
Was ist Bioinformatik?
 9. Kurstag: Bioinformatik Der Begriff "Bioinformatik" wurde 1989 erstmals von D.R. Masys im JOURNAL OF RESEARCH OF THE NATIONAL INSTITUTE OF STANDARDS AND TECHNOLOGY erwähnt. Was ist Bioinformatik? Die
9. Kurstag: Bioinformatik Der Begriff "Bioinformatik" wurde 1989 erstmals von D.R. Masys im JOURNAL OF RESEARCH OF THE NATIONAL INSTITUTE OF STANDARDS AND TECHNOLOGY erwähnt. Was ist Bioinformatik? Die
BCDS - Biochemische Datenbanken und Software
 BCDS - Biochemische Datenbanken und Software Seminarinhalte Bioinformatische Genom- und Proteomanalyse Literaturrecherche und Zitation Naturwissenschaftliche Software Termine 25. Mai, 1. Juni, 8. Juni,
BCDS - Biochemische Datenbanken und Software Seminarinhalte Bioinformatische Genom- und Proteomanalyse Literaturrecherche und Zitation Naturwissenschaftliche Software Termine 25. Mai, 1. Juni, 8. Juni,
MOL.504 Analyse von DNA- und Proteinsequenzen. Übungsaufgaben Datenbanken und Informationssysteme
 MOL.504 Analyse von DNA- und Proteinsequenzen Übungsaufgaben Datenbanken und Informationssysteme Ü1 Tutorial für NCBI NCBI Nucleotide: Suche nach cellobiose dehydrogenase fungi Ü1 Tutorial für NCBI NCBI
MOL.504 Analyse von DNA- und Proteinsequenzen Übungsaufgaben Datenbanken und Informationssysteme Ü1 Tutorial für NCBI NCBI Nucleotide: Suche nach cellobiose dehydrogenase fungi Ü1 Tutorial für NCBI NCBI
Humane Genotyp-Phänotyp-Datenbanken: Ein Statusbericht
 Workshop: Datenbank genomischer Varianten für die klinische Anwendung und die medizinische Forschung Essen 19. März 2014 Humane Genotyp-Phänotyp-Datenbanken: Ein Statusbericht Thomas Bettecken Max-Planck-Institut
Workshop: Datenbank genomischer Varianten für die klinische Anwendung und die medizinische Forschung Essen 19. März 2014 Humane Genotyp-Phänotyp-Datenbanken: Ein Statusbericht Thomas Bettecken Max-Planck-Institut
Individuelle Genomsequenzen Aussichten für die Tierzucht
 Individuelle Genomsequenzen Aussichten für die Tierzucht Ruedi Fries WZW / Lehrstuhl für Tierzucht Agrarw. Symposium - 1 Auswirkungen der Genomischen Revolution auf die Tierzucht (und Pflanzenzucht) Agrarw.
Individuelle Genomsequenzen Aussichten für die Tierzucht Ruedi Fries WZW / Lehrstuhl für Tierzucht Agrarw. Symposium - 1 Auswirkungen der Genomischen Revolution auf die Tierzucht (und Pflanzenzucht) Agrarw.
Zeitreise in die Erdgeschichte
 Zeitreise in die Erdgeschichte 1. Einschätzen des Alters der Erde und der Organismen: a) Wann ist die Erde entstanden? vor 5,7 Millionen Jahren vor 4,5 Milliarden Jahren vor 750 Millionen Jahren vor 250.000
Zeitreise in die Erdgeschichte 1. Einschätzen des Alters der Erde und der Organismen: a) Wann ist die Erde entstanden? vor 5,7 Millionen Jahren vor 4,5 Milliarden Jahren vor 750 Millionen Jahren vor 250.000
Molekulargenetik der Eukaryoten WS 2014/15, VL 10. Erwin R. Schmidt Institut für Molekulargenetik
 Molekulargenetik der Eukaryoten WS 2014/15, VL 10 Erwin R. Schmidt Institut für Molekulargenetik Replikationsgabel bei Prokaryoten Replikationsgabel bei Eukaryoten Pol e Pol d GINS (Go, Ichi, Nii, and
Molekulargenetik der Eukaryoten WS 2014/15, VL 10 Erwin R. Schmidt Institut für Molekulargenetik Replikationsgabel bei Prokaryoten Replikationsgabel bei Eukaryoten Pol e Pol d GINS (Go, Ichi, Nii, and
Biochemie Vorlesung Die ersten 100 Seiten
 Biochemie Vorlesung 11-15 Die ersten 100 Seiten 1. Unterschiede der Zellen Eukaryoten- Prokaryoten Eukaryoten: - Keine Zellwand - Intrazelluläre Membransysteme - Kernhülle mit 2 Membranen und Kernporen
Biochemie Vorlesung 11-15 Die ersten 100 Seiten 1. Unterschiede der Zellen Eukaryoten- Prokaryoten Eukaryoten: - Keine Zellwand - Intrazelluläre Membransysteme - Kernhülle mit 2 Membranen und Kernporen
Über die evolutionäre Entwicklung eines Metabewusstseins durch die Existenz des Internets. Franz-Josef Schmitt
 Über die evolutionäre Entwicklung eines Metabewusstseins durch die Existenz des Internets Franz-Josef Schmitt Inhalt Biophysik Evolution Metastrukturen Metamaterialien Metaorganismen Evolution des Internets
Über die evolutionäre Entwicklung eines Metabewusstseins durch die Existenz des Internets Franz-Josef Schmitt Inhalt Biophysik Evolution Metastrukturen Metamaterialien Metaorganismen Evolution des Internets
1. Beschreiben Sie die Rolle der folgenden Proteine bei der DNA- Replikation in E. coli:
 1. Beschreiben Sie die Rolle der folgenden Proteine bei der DNA- Replikation in E. coli: Übung 7 - DnaA bindet an 13 bp DNA Sequenz (DnaA Box, 5 Wiederholungen bei E. coli) im oric ori wird in AT reicher
1. Beschreiben Sie die Rolle der folgenden Proteine bei der DNA- Replikation in E. coli: Übung 7 - DnaA bindet an 13 bp DNA Sequenz (DnaA Box, 5 Wiederholungen bei E. coli) im oric ori wird in AT reicher
Schulinternes Fachcurriculum Biologie Elsensee-Gymnasium Quickborn
 Schulinternes Fachcurriculum Biologie Elsensee-Gymnasium Quickborn 1 für die Sekundarstufe I Klassenstufe 5 Optional: Hund oder Katze; Rind oder 10 F 1.4, F2.4, Pferd F2.6, F3.2 -Tierhaltung und Tierpflege
Schulinternes Fachcurriculum Biologie Elsensee-Gymnasium Quickborn 1 für die Sekundarstufe I Klassenstufe 5 Optional: Hund oder Katze; Rind oder 10 F 1.4, F2.4, Pferd F2.6, F3.2 -Tierhaltung und Tierpflege
Das Human-Genom und seine sich abzeichnende Dynamik
 Das Human-Genom und seine sich abzeichnende Dynamik Matthias Platzer Genomanalyse Leibniz Institut für Altersforschung - Fritz-Lipmann Institut (FLI) Humangenom - Sequenzierung 1. Methode 2. Ergebnisse
Das Human-Genom und seine sich abzeichnende Dynamik Matthias Platzer Genomanalyse Leibniz Institut für Altersforschung - Fritz-Lipmann Institut (FLI) Humangenom - Sequenzierung 1. Methode 2. Ergebnisse
Datenbanken in der Bioinformatik
 Datenbanken in der Bioinformatik Kapitel 1 Motivation und Grundlagen http://dbs.uni-leipzig.de Institut für Informatik Vorläufiges Inhaltsverzeichnis 1. Motivation und Grundlagen 2. Klassifizierung von
Datenbanken in der Bioinformatik Kapitel 1 Motivation und Grundlagen http://dbs.uni-leipzig.de Institut für Informatik Vorläufiges Inhaltsverzeichnis 1. Motivation und Grundlagen 2. Klassifizierung von
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
Die Zelle Eine chemische Fabrik im Nanomaßstab
 Die Zelle Eine chemische Fabrik im Nanomaßstab Peter Schuster Institut für Theoretische Chemie, Universität Wien, Österreich und Österreichische Akademie der Wissenschaften Höhere Technische Bundeslehranstalt
Die Zelle Eine chemische Fabrik im Nanomaßstab Peter Schuster Institut für Theoretische Chemie, Universität Wien, Österreich und Österreichische Akademie der Wissenschaften Höhere Technische Bundeslehranstalt
Informationsgehalt von DNA
 Informationsgehalt von DNA Topics Genes code, gene organisation, signals, gene detection Genomes genome organisation, nucleotide patterns, junk DNA DNA als Informationsträger DNA Building Blocks Desoxyribose
Informationsgehalt von DNA Topics Genes code, gene organisation, signals, gene detection Genomes genome organisation, nucleotide patterns, junk DNA DNA als Informationsträger DNA Building Blocks Desoxyribose
Mikrobielle Arten und Taxonomie
 Mikrobielle Arten und Taxonomie - Was ist eine Art? Grundsatz in der Biologie: Kreuzbarkeit, d.h. sexuelle Vermehrung - Bacteria und Archaea vermehren sich asexuell; außerdem horizontaler Gentransfer Hoffnung
Mikrobielle Arten und Taxonomie - Was ist eine Art? Grundsatz in der Biologie: Kreuzbarkeit, d.h. sexuelle Vermehrung - Bacteria und Archaea vermehren sich asexuell; außerdem horizontaler Gentransfer Hoffnung
Evolution und Entwicklung
 Evolution und Entwicklung Wie aus einzelnen Zellen die Menschen wurden: Phylogenese Klassische Genetik: Mendel Moderne Genetik: Watson & Crick Wie aus einer einzigen Zelle ein Mensch wird: Ontogenese Vererbung
Evolution und Entwicklung Wie aus einzelnen Zellen die Menschen wurden: Phylogenese Klassische Genetik: Mendel Moderne Genetik: Watson & Crick Wie aus einer einzigen Zelle ein Mensch wird: Ontogenese Vererbung
MOL.504 Analyse von DNA- und Proteinsequenzen
 MOL.504 Analyse von DNA- und Proteinsequenzen Kurs 1 Monika Oberer, Karl Gruber MOL.504 Modul-Übersicht Einführung, Datenbanken BLAST-Suche, Sequenzalignment Proteinstrukturen Virtuelles Klonieren Abschlusstest
MOL.504 Analyse von DNA- und Proteinsequenzen Kurs 1 Monika Oberer, Karl Gruber MOL.504 Modul-Übersicht Einführung, Datenbanken BLAST-Suche, Sequenzalignment Proteinstrukturen Virtuelles Klonieren Abschlusstest
Genom-Evolution in Wirts-adaptierten Bakterien Genome evolution in host-adapted bacteria
 Genom-Evolution in Wirts-adaptierten Bakterien Genome evolution in host-adapted bacteria Schuster, Stephan C. Max-Planck-Institut für Entwicklungsbiologie, Tübingen Korrespondierender Autor E-Mail: stephan.schuster@tuebingen.mpg.de
Genom-Evolution in Wirts-adaptierten Bakterien Genome evolution in host-adapted bacteria Schuster, Stephan C. Max-Planck-Institut für Entwicklungsbiologie, Tübingen Korrespondierender Autor E-Mail: stephan.schuster@tuebingen.mpg.de
DiversiLab TM Schnelle und reproduzierbare Stammtypisierung
 DIVERSILABTM DiversiLab TM Schnelle und reproduzierbare Stammtypisierung 2/24 Weshalb Stammtypisierung? Eine Stammtypisierung dient nicht zur Identifizierung eines Erregers sondern um abzuklären, ob zwei
DIVERSILABTM DiversiLab TM Schnelle und reproduzierbare Stammtypisierung 2/24 Weshalb Stammtypisierung? Eine Stammtypisierung dient nicht zur Identifizierung eines Erregers sondern um abzuklären, ob zwei
Einführung Molekulare Bioinformatik
 Einführung Molekulare Bioinformatik Bernhard Haubold 22. Oktober 2013 Übersicht Was ist Bioinformatik? Kursstruktur Was ist Bioinformatik? Geschichtliche Entwicklung Information: Speicherung & Übertragung
Einführung Molekulare Bioinformatik Bernhard Haubold 22. Oktober 2013 Übersicht Was ist Bioinformatik? Kursstruktur Was ist Bioinformatik? Geschichtliche Entwicklung Information: Speicherung & Übertragung
Vorbesprechung Seminar Biomedical Informatics
 Vorbesprechung Martin Dugas und Xiaoyi Jiang Institut für Informatik Sommersemester 2016 Organisation Vorlage: Englischsprachige Publikation Vortrag: ca. 30min + 15min Diskussion, Blockseminar Anfang/Mitte
Vorbesprechung Martin Dugas und Xiaoyi Jiang Institut für Informatik Sommersemester 2016 Organisation Vorlage: Englischsprachige Publikation Vortrag: ca. 30min + 15min Diskussion, Blockseminar Anfang/Mitte
URSPRUNG UND EVOLUTION VON ARCHAEEN - EINE ABHANDLUNG AUF STAND VON 2006
 URSPRUNG UND EVOLUTION VON ARCHAEEN - EINE ABHANDLUNG AUF STAND VON 2006 Patrick Dörner Seminar Modul 13 Wintersemester 14/15 Johannes Gutenberg Universität Mainz GLIEDERUNG 1. Einführung Archaea 2. Die
URSPRUNG UND EVOLUTION VON ARCHAEEN - EINE ABHANDLUNG AUF STAND VON 2006 Patrick Dörner Seminar Modul 13 Wintersemester 14/15 Johannes Gutenberg Universität Mainz GLIEDERUNG 1. Einführung Archaea 2. Die
Vorlesungsthemen Mikrobiologie
 Vorlesungsthemen Mikrobiologie 1. Einführung in die Mikrobiologie B. Bukau 2. Zellaufbau von Prokaryoten B. Bukau 3. Bakterielles Wachstum und Differenzierung B. Bukau 4. Bakterielle Genetik und Evolution
Vorlesungsthemen Mikrobiologie 1. Einführung in die Mikrobiologie B. Bukau 2. Zellaufbau von Prokaryoten B. Bukau 3. Bakterielles Wachstum und Differenzierung B. Bukau 4. Bakterielle Genetik und Evolution
DNA Sequenzierung. Transkriptionsstart bestimmen PCR
 10. Methoden DNA Sequenzierung Transkriptionsstart bestimmen PCR 1. Erklären Sie das Prinzip der Sanger Sequenzierung. Klären Sie dabei folgende Punkte: a) Welche besondere Art von Nukleotiden wird verwendet
10. Methoden DNA Sequenzierung Transkriptionsstart bestimmen PCR 1. Erklären Sie das Prinzip der Sanger Sequenzierung. Klären Sie dabei folgende Punkte: a) Welche besondere Art von Nukleotiden wird verwendet
Genetik und Eugenik II. 1945 bis heute
 Genetik und Eugenik II 1945 bis heute Literatur James D. Watson, Die Doppel-Helix (1969, dt. 2001), Auszug. Walter Gilbert, Das Genom - Eine Zukunftsvision (Original: A Vision of the Grail), In: Daniel
Genetik und Eugenik II 1945 bis heute Literatur James D. Watson, Die Doppel-Helix (1969, dt. 2001), Auszug. Walter Gilbert, Das Genom - Eine Zukunftsvision (Original: A Vision of the Grail), In: Daniel
2.2. Peptide. Peptide entstehen durch Kondensation der a-carboxylgruppe einer Aminosäure mit der a-aminogruppe einer anderen Aminosäure
 2.2. Peptide Peptide entstehen durch Kondensation der a-carboxylgruppe einer Aminosäure mit der a-aminogruppe einer anderen Aminosäure Peptid: bis zu ~30 linear über Peptidbindung verknüpfte Aminosäuren
2.2. Peptide Peptide entstehen durch Kondensation der a-carboxylgruppe einer Aminosäure mit der a-aminogruppe einer anderen Aminosäure Peptid: bis zu ~30 linear über Peptidbindung verknüpfte Aminosäuren
Archiv der Jahrestagungen der VAAM
 Archiv der Jahrestagungen der VAAM Bochum, 8.-11.3.2009 Mitglieder: 3229 Teilnehmer: 1342 Themen: Microbial Cell Biology :: Green Microbiology :: Sensory and Regulatory RNA :: Host-microbe Interactions
Archiv der Jahrestagungen der VAAM Bochum, 8.-11.3.2009 Mitglieder: 3229 Teilnehmer: 1342 Themen: Microbial Cell Biology :: Green Microbiology :: Sensory and Regulatory RNA :: Host-microbe Interactions
Genetik - The Human Genome Project. Überblick über die Genetik. Die gesamte Erbinformation eines Menschen befindet sich in jedem Zellkern
 Genetik - The Human Genome Project Überblick über die Genetik Die gesamte Erbinformation eines Menschen befindet sich in jedem Zellkern seines Körpers. 1 2 Im Organismus müsssen nun ständig Enzyme u. a.
Genetik - The Human Genome Project Überblick über die Genetik Die gesamte Erbinformation eines Menschen befindet sich in jedem Zellkern seines Körpers. 1 2 Im Organismus müsssen nun ständig Enzyme u. a.
MBI: Sequenz-Vergleich mit Alignment
 MBI: Sequenz-Vergleich mit Alignment Bernhard Haubold 28. Oktober 2014 Wiederholung: Was ist Bioinformatik? Historische Übersicht; CABIOS Bioinformatics Gemeinsames Thema: Information in vivo DNA Epigenetik
MBI: Sequenz-Vergleich mit Alignment Bernhard Haubold 28. Oktober 2014 Wiederholung: Was ist Bioinformatik? Historische Übersicht; CABIOS Bioinformatics Gemeinsames Thema: Information in vivo DNA Epigenetik
Erster Baum genetisch sequenziert Genetische Veränderung geplant - Ökologen warnen vor Gentech- Pflanzen
 Erster Baum genetisch sequenziert Genetische Veränderung geplant - Ökologen warnen vor Gentech- Pflanzen Das erste Genom eines Baumes wurde nach Angaben des Wissenschaftsmagazins Science nun fertig entschlüsselt.
Erster Baum genetisch sequenziert Genetische Veränderung geplant - Ökologen warnen vor Gentech- Pflanzen Das erste Genom eines Baumes wurde nach Angaben des Wissenschaftsmagazins Science nun fertig entschlüsselt.
Anabole Prozesse in der Zelle
 Anabole Prozesse in der Zelle DNA Vermehrung RNA Synthese Protein Synthese Protein Verteilung in der Zelle Ziel: Zellteilung (Wachstum) und Differenzierung (Aufgabenteilung im Organismus). 2016 Struktur
Anabole Prozesse in der Zelle DNA Vermehrung RNA Synthese Protein Synthese Protein Verteilung in der Zelle Ziel: Zellteilung (Wachstum) und Differenzierung (Aufgabenteilung im Organismus). 2016 Struktur
Die Evolution. Molekularer Netzwerke. Sarah A. Teichmann
 Die Evolution Molekularer Netzwerke Sarah A. Teichmann Embryonale Entwicklung des Seeigels (Strongylocentrotus purpuratus) Systembiologie: Biologen als molekulare Ingenieure Schaltkreise der embryonalen
Die Evolution Molekularer Netzwerke Sarah A. Teichmann Embryonale Entwicklung des Seeigels (Strongylocentrotus purpuratus) Systembiologie: Biologen als molekulare Ingenieure Schaltkreise der embryonalen
Versuch 2 DNA Reparatur und Rekombination
 Versuch 2 DNA Reparatur und Rekombination Warum ist DNA-Reparatur wichtig? Genetische Variation ist doch der Motor der Evolution. Mutationen durch Externe Einflüsse: Ionisierende Strahlung Chemotherapeutika
Versuch 2 DNA Reparatur und Rekombination Warum ist DNA-Reparatur wichtig? Genetische Variation ist doch der Motor der Evolution. Mutationen durch Externe Einflüsse: Ionisierende Strahlung Chemotherapeutika
Kaninchen: 1 cagattgaggagagcaccaccatcgtcacctcgcagttggcggaggtcagcgcagccgag 60
 Ergebnisse 6 3. Ergebnisse 3. Charakterisierung der zelllinienspezifischen cdn Die Entwicklung zweier Zelllinien, des epithelialen Trophoblasten und des pluripotenten Embryoblasten, ist der erste Differenzierungsschritt
Ergebnisse 6 3. Ergebnisse 3. Charakterisierung der zelllinienspezifischen cdn Die Entwicklung zweier Zelllinien, des epithelialen Trophoblasten und des pluripotenten Embryoblasten, ist der erste Differenzierungsschritt
Einführung in die Bioinformatik
 Einführung in die Bioinformatik Kay Nieselt Integrative Transkriptomik Zentrum für Bioinformatik Tübingen Kay.Nieselt@uni-tuebingen.de SS 2011 8. Biologische Netzwerke - Gut vernetzt hält besser Überblick
Einführung in die Bioinformatik Kay Nieselt Integrative Transkriptomik Zentrum für Bioinformatik Tübingen Kay.Nieselt@uni-tuebingen.de SS 2011 8. Biologische Netzwerke - Gut vernetzt hält besser Überblick
Molekulargenetik Biologie am Inhaltsverzeichnis Die Begriffe DNA, Nukleotid, Gen, Chromosom und Epigenom definieren...
 Molekulargenetik Inhaltsverzeichnis Die Begriffe DNA, Nukleotid, Gen, Chromosom und Epigenom definieren... 2 Beschreiben, wie die DNA aufgebaut ist... 3 Den Ablauf der Replikation erklären und dabei die
Molekulargenetik Inhaltsverzeichnis Die Begriffe DNA, Nukleotid, Gen, Chromosom und Epigenom definieren... 2 Beschreiben, wie die DNA aufgebaut ist... 3 Den Ablauf der Replikation erklären und dabei die
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Vorbemerkung für die Erlangung des Testats: Bearbeiten Sie die unten gestellten Aufgaben
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Vorbemerkung für die Erlangung des Testats: Bearbeiten Sie die unten gestellten Aufgaben
4.9.7 Konstruktion der Suffixbäume
 .9.7 Konstruktion der Suffixbäume Beipiel: xabxa (siehe Abbildung.27) Man beginnt mit der Konstruktion eines Suffixbaumes für gesamten String und schreibt eine 1 am Blatt, weil der Suffix xabxa an der
.9.7 Konstruktion der Suffixbäume Beipiel: xabxa (siehe Abbildung.27) Man beginnt mit der Konstruktion eines Suffixbaumes für gesamten String und schreibt eine 1 am Blatt, weil der Suffix xabxa an der
Einführung in die Bioinformatik
 Einführung in die Bioinformatik Kay Nieselt Integrative Transkriptomik Zentrum für Bioinformatik Tübingen Kay.Nieselt@uni-tuebingen.de SS 2011 1. Was ist Bioinformatik? Ablauf und Formales Ringvorlesung
Einführung in die Bioinformatik Kay Nieselt Integrative Transkriptomik Zentrum für Bioinformatik Tübingen Kay.Nieselt@uni-tuebingen.de SS 2011 1. Was ist Bioinformatik? Ablauf und Formales Ringvorlesung
Procyte Eucyte Organell Aufgabe Zellorganell Autotrophe Stellen Nährstoffe selbst her Organismen Pflanzen Fotosynthese Bakterien Chemosynthese
 Procyte (die) Eucyte (die) Zellorganell (das; -organellen) Organell Zellkern Ribosomen Mitochondrien Chloroplasten Endoplasmatisches Retikulum (ER) Golgiapparat (Dictyosom) Membran Zellwand Vakuole Aufgabe
Procyte (die) Eucyte (die) Zellorganell (das; -organellen) Organell Zellkern Ribosomen Mitochondrien Chloroplasten Endoplasmatisches Retikulum (ER) Golgiapparat (Dictyosom) Membran Zellwand Vakuole Aufgabe
Grundwissen 8. Klasse gemäß Lehrplan Gymnasium Bayern G8
 Grundwissen 8. Klasse gemäß Lehrplan Gymnasium Bayern G8 Biologie 1. Einfache Organisationsstufen von Lebewesen Prokaryoten Einzellige Lebewesen, die keinen Zellkern und keine membranumhüllten Zellorganellen
Grundwissen 8. Klasse gemäß Lehrplan Gymnasium Bayern G8 Biologie 1. Einfache Organisationsstufen von Lebewesen Prokaryoten Einzellige Lebewesen, die keinen Zellkern und keine membranumhüllten Zellorganellen
Institut für Biochemie und Molekulare Medizin. Lecture 1 Translational components. Michael Altmann FS 2011
 Institut für Biochemie und Molekulare Medizin Lecture 1 Translational components Michael Altmann FS 2011 Gene Expression Fliessdiagramm der eukaryotischen Genexpression Die Expression eines Gens kann auf
Institut für Biochemie und Molekulare Medizin Lecture 1 Translational components Michael Altmann FS 2011 Gene Expression Fliessdiagramm der eukaryotischen Genexpression Die Expression eines Gens kann auf
Mikrobiom und seine Bedeutung für die Niere
 Mikrobiom und seine Bedeutung für die Niere Britta Siegmund Charité, Campus Benjamin Franklin Medizinische Klinik m.s. Gastroenterologie/ Rheumatologie/ Infektiologie Berlin Mikrobiota Darm Metagenom Genetische
Mikrobiom und seine Bedeutung für die Niere Britta Siegmund Charité, Campus Benjamin Franklin Medizinische Klinik m.s. Gastroenterologie/ Rheumatologie/ Infektiologie Berlin Mikrobiota Darm Metagenom Genetische
Alignments & Datenbanksuchen
 WS2017/2018 Genomforschung und Sequenzanalyse - Einführung in Methoden der Bioinformatik- Thomas Hankeln Alignments & Datenbanksuchen 1 break-thru Doolittle et al. 1983, Waterfield et al. 1983 > DB-Suche...
WS2017/2018 Genomforschung und Sequenzanalyse - Einführung in Methoden der Bioinformatik- Thomas Hankeln Alignments & Datenbanksuchen 1 break-thru Doolittle et al. 1983, Waterfield et al. 1983 > DB-Suche...
UNIVERSITÄTSKLINIKUM Schleswig-Holstein. Sequenzierung. Norbert Arnold. Dept. Gynecology and Obstetrics Oncology Laboratory
 Sequenzierung Norbert Arnold Neue Sequenziertechnologien (seit 2005) Next Generation Sequenzierung (NGS, Erste Generation) Unterschiedliche Plattformen mit unterschiedlichen Strategien Roche 454 (basierend
Sequenzierung Norbert Arnold Neue Sequenziertechnologien (seit 2005) Next Generation Sequenzierung (NGS, Erste Generation) Unterschiedliche Plattformen mit unterschiedlichen Strategien Roche 454 (basierend
Die spiralförmige Strickleiter des Lebens
 Die spiralförmige Strickleiter des Lebens Ursula Loos Vor genau 50 Jahren beschrieben James D.Watson und Francis C.Crick mit der Doppelhelix die Raumstruktur der DNS ein paar Jahre später sind sie hierfür
Die spiralförmige Strickleiter des Lebens Ursula Loos Vor genau 50 Jahren beschrieben James D.Watson und Francis C.Crick mit der Doppelhelix die Raumstruktur der DNS ein paar Jahre später sind sie hierfür
Einführung Molekulare Bioinformatik
 Einführung Molekulare Bioinformatik Bernhard Haubold 21. Oktober 2014 Übersicht Was ist Bioinformatik? Kursstruktur Was ist Bioinformatik? Geschichtliche Entwicklung Information: Speicherung & Übertragung
Einführung Molekulare Bioinformatik Bernhard Haubold 21. Oktober 2014 Übersicht Was ist Bioinformatik? Kursstruktur Was ist Bioinformatik? Geschichtliche Entwicklung Information: Speicherung & Übertragung
Grundlagen der Bioinformatik Assignment 3: Hierarchical Clustering SS Yvonne Lichtblau/Johannes Starlinger
 Grundlagen der Bioinformatik Assignment 3: Hierarchical Clustering SS 2017 Yvonne Lichtblau/Johannes Starlinger Presentations Assignment 2 Yvonne Lichtblau Übungen Grundlagen der Bioinformatik SS 2017
Grundlagen der Bioinformatik Assignment 3: Hierarchical Clustering SS 2017 Yvonne Lichtblau/Johannes Starlinger Presentations Assignment 2 Yvonne Lichtblau Übungen Grundlagen der Bioinformatik SS 2017
Veranstaltungen, SWS, ECTS, Prüfungsdauer
 Anhang 1: 1 2 3 4 5 6 7 8 9 10 Veranstaltungen, SWS, ECTS, Pflichtveranstaltungen in Grundstudium Veranstaltung SWS ECTS (Klausur) (mündl.) Einführung in die Informatik I (LMU/TUM Alt) # 4V+3Ü 9 135-225
Anhang 1: 1 2 3 4 5 6 7 8 9 10 Veranstaltungen, SWS, ECTS, Pflichtveranstaltungen in Grundstudium Veranstaltung SWS ECTS (Klausur) (mündl.) Einführung in die Informatik I (LMU/TUM Alt) # 4V+3Ü 9 135-225
Einführung in die Marinen Umweltwissenschaften
 Einführung in die Marinen Umweltwissenschaften www.icbm.de/pmbio Mikrobiologische Grundlagen - Rolle der Mikroorganismen in der Natur - Beispiel Meer - Biogeochemie, Mikrobielle Ökologie, Umweltmikrobiologie
Einführung in die Marinen Umweltwissenschaften www.icbm.de/pmbio Mikrobiologische Grundlagen - Rolle der Mikroorganismen in der Natur - Beispiel Meer - Biogeochemie, Mikrobielle Ökologie, Umweltmikrobiologie
DNA-Synthese in vivo und in vitro
 DNA-Synthese in vivo und in vitro 4 Einführung Replikation der DNA Entwindung der DNA Priming der DNA-Synthese Struktur und Funktion der DNA-Polymerase Synthese des Folgestranges Fehlpaarungsreparatur
DNA-Synthese in vivo und in vitro 4 Einführung Replikation der DNA Entwindung der DNA Priming der DNA-Synthese Struktur und Funktion der DNA-Polymerase Synthese des Folgestranges Fehlpaarungsreparatur
Ontologien und Ontologiesprachen
 Ontologien und Ontologiesprachen Semantische Datenintegration SoSe2005 Uni Bremen Yu Zhao Gliederung 1. Was ist Ontologie 2. Anwendungsgebiete 3. Ontologiesprachen 4. Entwicklung von Ontologien 5. Zusammenfassung
Ontologien und Ontologiesprachen Semantische Datenintegration SoSe2005 Uni Bremen Yu Zhao Gliederung 1. Was ist Ontologie 2. Anwendungsgebiete 3. Ontologiesprachen 4. Entwicklung von Ontologien 5. Zusammenfassung
