Diskussion 62 6 DISKUSSION
|
|
|
- Walther Schmitz
- vor 7 Jahren
- Abrufe
Transkript
1 Diskussion 62 6 DISKUSSION Kartierungsergebnisse Sowohl die Analyse von Deletionssyndromen, wie dem WAGR-Syndrom, als auch Beobachtungen von Allelverlusten der Region 11p in verschiedenen Tumoren lassen neben den bereits kartierten Genen auf weitere bisher unbekannte Gene schließen, die die genetische Ursache dieser Krankheiten klären können. Eine detaillierte Kartierung mit dem Ziel der Sequenzierung und der daraus resultierenden Identifizierung neuer Gene dieser Region ist daher von erheblichem Interesse. Die Voraussetzung für eine Sequenzierung sind Contigs, die möglichst vollständig und in hoher Abdeckung die genomische Sequenz repräsentieren. Zu Beginn der Arbeit existierte bereits ein Contig bestehend aus YAC-Klonen, die 8 Mb der Region 11p vollständig abdecken (Gawin et al. 1995). Allerdings sind die Klone des YAC-Vektorsystems ungeeignet für eine spätere Sequenzierung. Gründe hierfür liegen in der Größe der YAC-Inserts. Diese bewegt sich durchschnittlich zwischen 300 kb und 1 Mb. Durch die relativ hohe Instabilität der Inserts kommt es häufig zum teilweisen Verlust des Inserts oder zu Chimärität vieler YAC-Klone. Sie können verschiedene Inserts besitzen, die von unterschiedlichen Bereichen der genomischen Sequenz stammen. Das System des PAC-Vektors, das für eine Feinkartierung des Chromosomenabschnitts 11p13 gewählt wurde, erweist sich gegenüber dem YAC-Vektorsytem als vorteilhaft. Die Insertgröße der PAC-Klone liegt durchschnittlich bei 120 kb, woraus eine höhere Stabilität des PAC-Inserts im Vergleich zum YAC-Klon resultiert. Letztendlich wurde auch ein System benötigt, dessen technische Handhabung vergleichsweise einfach ist. PAC- DNA ist relativ leicht zu isolieren und die Anzucht von E.coli ist wesentlich problemloser als die der Hefezellen Saccharomyces cerevisiae, in denen das YAC-Vektorsystem vermehrt wird. Als genomische Bibliothek stand die PAC-Bank RPCI 1,3-5, die auf High Density Grid Filtern aufgebracht war, zur Verfügung (Ioannou et al. 1994). Die theoretische Abdeckung der einzelnen PAC-Banken reichte vom Drei- bis Sechsfachen des gesamten menschlichen Genoms. Da mehrere dieser Banken zeitgleich benutzt wurden, addieren sich die jeweiligen Einzelwerte auf eine insgesamt 16-fache Abdeckung der verwendeten genomischen PAC-Bibliothek. Je höher die Abdeckung der Bibliothek, die für ein Screening benutzt wird, ist, desto größer ist auch die Wahrscheinlichkeit ein lückenloses Contig mit den identifizierten Klonen erstellen zu können. Für die Identifizierung 11p13-spezifischer PAC-Klone wurden Alu-PCR-Proben von YAC-Klonen aus dem YAC-Contig, das 11p abdeckt, benutzt. Dazu ergänzend wurden YAC-Endproben, sowie auf 11p13 lokalisierte Marker als Probe verwendet. Bei der späteren Analyse der hiermit erhaltenen PAC-Bibliothek konnte die Spezifität der Klone für die Region 11p13 nicht für alle PAC-Klone bestätigt werden. Dies galt für Klone, deren Endprobe keine zusätzlichen Klone identifizieren konnte und die außerdem mit keiner der 11p13-spezifischen Marker verifiziert werden konnten. Gründe hierfür liegen in Fehlerquellen bei der Auswertung der Koordinaten auf den High Density Grid Filtern. Die Klone waren zwar nach einem bestimmten Muster doppelt auf die Filter gestempelt, manche dieser Muster waren aber nicht deutlich voneinander zu unterscheiden. Für diese Muster ergaben sich bei der Auswertung theoretisch zwei Möglichkeiten der Koordinatenbestimmung. Ein weiterer Anteil der Klone wiederum zeigte ein positives Signal mit den meisten der verwendeten PAC-Endproben und Marker, oder die Hybridisierung mit deren Endproben erzeugte einen so hohen Hybridisierungshintergund, daß eine Auswertung dieser Ergebnisse nicht möglich war. Bei einem Teil dieser Klone konnte
2 Diskussion 63 nachgewiesen werden, daß sie kein Insert besaßen. Aufgrund der Größe des Inserts (~120 kb) bedeutet dies einen Replikationsvorteil des PAC-Vektors gegenüber Klonen mit Insert. Daraus resultiert eine stärkere Hybridisierung dieser Klone, was ein falsch positives Signal vortäuscht. Eine andere Erklärung für eine hohe Hintergrundhybridisierung ist ein hoher Gehalt an repetitiven Sequenzen. Liegen diese Sequenzen nahe der Klonierungsstelle, so werden diese bei der Generierung der Endproben mit amplifiziert. Bei der Hybridisierung auf die Filter mit den 11p13 spezifischen PAC-Klonen wurde zwar zur Absättigung repetitiver Sequenzen mit menschlicher DNA kompetiert, seltener im Genom vorkommende repetitive Sequenzen (low copy repeats) konnten mit dieser Methode allerdings nicht abgesättigt werden. Schließlich wurden Klone identifiziert, deren Spezifität für die Region 11p13 zwar bestätigt werden konnte, deren Inserts aber eine Deletion oder Insertion auwiesen. Eine Deletion wurde dann vermutet, wenn bei der Erstellung des Contigs ein positives Signal, das für diesen Klon aufgrund der übrigen Daten zu erwarten gewesen wäre, gefehlt hatte. Klone mit einer Insertion oder einem Doppelinsert wiederum zeigten positive Hybridisierungssignale in zwei oder mehreren unabhängigen Contigs und konnten demzufolge keiner dieser unterschiedlichen Regionen zugeordnet werden. Für die Erstellung des Contigs, dessen Klone für die Sequenzierung am Sanger Centre/UK herangezogen wurden, konnten letztendlich 113 Klone von 618 eindeutig miteinbezogen werden. Bis auf eine Ausnahme (104M13) waren dies PAC-Klone, bei denen keine Deletionen oder Insertionen bzw. Doppelinserts festgestellt werden konnten. 104M13 ist vermutlich deletiert, da er mit PAC-Enden überlappender Klone kein positives Hybridierungssignal zeigte, hingegen positiv für die beiden Marker D11S87 und WT1 war. Der scheinbar hohe Verlust von über 80 % der identifizierten 11p13 spezifischen PAC-Klone, die nicht in das endgültig erstellte Contig miteinbezogen wurden, ist darauf zurückzuführen, daß zu Beginn der Arbeit Hybridisierungsproben verwendet wurden, die außerhalb des fertiggestellten Contigs lagen. Die 107 mit diesen Proben identifizierten PAC-Klone wurden in die Statistik miteinbezogen, jedoch später nicht mehr bei der Konstruktion des Contigs berücksichtigt. Die Region der Größe von 3 Mb auf der Telomer-Seite des gezeigten Contigs, von der ein Teil der verwendeten Proben stammte, wurde von Beate Gawin weiter analysiert. Die Region einer Größe von etwa 0,6 Mb auf der Centromer-Seite des Markers D11S935 wurde nach Absprache mit Glenn Evans (University of Texas Southwestern) ebenfalls von weiteren Kartierungen im Rahmen dieser Arbeit ausgeschlossen. Für die 4,5 Mb zwischen dem Marker D11S935 und dem Gen PAX6 konnte ein Contig mit mehrfacher Abdeckung mit Ausnahme von fünf Regionen, die jeweils unter 50 kb liegen, erstellt werden. Eine mehrfache Abdeckung grenzt die Wahrscheinlichkeit von deletierten Klonen ein, da bei genügend hoher Hybridisierungsdichte Deletionen weniger häufig übersehen werden können. Um das mittels Hybridisierungsdaten erstellte PAC-Contig zu bestätigen, wurde in einem unabhängigen Ansatz von Holger Hummerich (Imperial College of Science, Medicine and Technology/UK) die Überlappung der Klone mittels Fingerprintanalysen überprüft. Nach einem Restriktionsverdau der PAC-DNA mit den Enzymen HindIII und Sau3AI wurden die erhaltenen Muster mit Hilfe des Programms FPC (V2.8.2) (Soderlund, Longden und Mott 1997) miteinander verglichen und daraus eine Überlappungswahrscheinlichkeit der Klone errechnet. Für Regionen mit hoher Abdeckung konnte die Überlappung in jedem Fall bestätigt werden. In Bereichen mit nur einfacher Abdeckung oder zwischen Klonen geringer Überlappung konnte mittels Fingerprintanalysen keine
3 Diskussion 64 signifikante Aussage getroffen werden. Die Überlappung wird an diesen Stellen jedoch durch die Hybridisierungsergebnisse aufrechterhalten. Hier wurden wie an den meisten Stellen des gesamten PAC-Contigs, die Hybridisierungsergebnisse aus den Koloniefilterhybridisierungen durch Ergebnisse aus den Hybridisierungen auf Southern Blots mit EcoRI verdauter PAC-DNA verifiziert. Für eine Sequenzierung des erstellten PAC-Contigs konnte ein minimal tiling path erstellt werden, das heißt, es wurden diejenigen Klone gewählt, die mit der geringsten Überlappung den gewünschten Bereich auf Chromosom 11p13 abdecken. Der hier gewählte minimal tiling path unterscheidet sich an einer Stelle von den vom Sanger Centre/UK vorgeschlagenen Klonen für eine spätere Sequenzierung. Der Klon 594L9 wurde vom Sanger Centre/UK aufgrund der Fingerprint-Daten, die von Holger Hummerich erstellt wurden, für die Sequenzierung gewählt. Da für diesen Klon keine Hybridisierungsdaten zur Verfügung stehen, erscheint dieser Klon nicht in dem unter Abbildung 8 gezeigten Contig. Strategien zur Identifizierung neuer Gene Auf der Grundlage des hier erstellten PAC-Contigs können bekannte Gene genau lokalisiert werden, wie für die beiden Gene ELF5 und PDX1 gezeigt wurde. Darüber hinaus können zusätzlich neue Gene innerhalb einer Region von 4,5 Mb Länge identifiziert werden. Um nach neuen Transkripten zu suchen, wurde ein experimenteller Weg über das Exontrapping gewählt. Ergänzend hierzu wurde eine computergestützte Suche nach Genen in den vom Sanger Centre/UK fertiggestellten Sequenzen durchgeführt. Eine Identifizierung neuer Transkripte mit Hilfe des Exonstrappings ist sinnvoll, da zum einen durch die in silico Analyse gefundene Gene bestätigt werden sollten. Dies gilt vor allem für Exonvorhersagen, für die keine Übereinstimmung mit einem EST-Klon oder einem bekannten Gen gefunden werden kann. Hier stellt das Exontrapping eine Möglichkeit der Verifizierung dar. Zum anderen können über eine computergestütze Analyse von DNA-Sequenzen nicht alle Exons erfaßt werden, da Exon-Intron-Strukturen mit einer Wahrscheinlichkeit von nur 60 % vorhergesagt werden (Segovia 1998). Aus diesem Grund ist es schwierig, diejenigen Transkripte über eine computergestützte Analyse zu identifizieren, die keine Ähnlichkeiten zu EST-Klonen oder anderen aus der Datenbank bekannten Sequenzen aufweisen. Eine Isolierung dieser Exons ist oft nur auf dem experimentellen Weg möglich. In der vorliegenden Arbeit wurde für das Exontrapping der Vektor pspl3-b verwendet, mit dem interne Exons in genomischer DNA identifiziert werden können. Neben Klonen, die ein potentielles Exon aus dem zuvor klonierten PAC-Klon enthielten, wurde eine hohe Anzahl an Artefakten erhalten. Diese enthielten entweder kein Intron (ca. 33 %), ein Intron mit Sequenzen aus dem pspl3-b-vektor (ca. 34 %), Introns mit repetitiven Sequenzen (Alu) oder Sequenzen aus E. coli. Fehlerquellen für das Auftreten von Artefaktklonen liegen in erster Linie am Vorhandensein kryptischer Spleißstellen, entweder in der eingesetzten genomischen DNA selbst, woraus möglicherweise die Inserts mit repetitiver DNA stammen, oder im pspl3-b-vektor. Ein kryptisches Exon, das bereits im pspl3- Vektor beschrieben wurde, wurde allerdings im pspl3-b Vektor eliminiert. Die von Burn et al. (1995) beobachtete Häufigkeit von Artefaktklonen mit einem pspl3-insert lag für den pspl3-b-vektor unter 1 % für pspl3 zwischen 5 und 46 %. Allerdings konnte diese niedrige Rate an Artefaktklonen hier nicht bestätigt werden.
4 Diskussion 65 Trotz der hohen Zahl an Artefakten, die jedoch eindeutig von positiven Klonen unterschieden werden konnten, wurden 35 Exons aus einer Region von etwa 700 kb detektiert, von denen 23 ein offenes Leseraster aufwiesen. Drei der identifizierten Exons stammen aus Genen, die zuvor schon auf diese PAC-Klone lokalisiert worden waren. Dies kann als eine Positivkontrolle für die angewandte Methode angesehen werden. Zur weiteren Kontrolle besteht nach Abschluß der Sequenzierung der PAC-Klone die Möglichkeit des Vergleichs mit den Sequenzen der identifizierten Exons. Mit einem überwiegenden Teil der isolierten Exons konnten keine Ähnlichkeiten zu EST-Klonen gefunden werden. Ein Grund kann in der Verwendung des pspl3-b-vektors liegen, mit dem grundsätzlich nur interne Exons isoliert werden. Da bei der Herstellung der cdna-banken Primer, die an das PolyA-Ende der mrna binden, verwendet werden, sind Klone, die das 3 -Ende eines Gens repräsentieren, in der Überzahl. Folglich stehen für interne Exons langer Transkripte häufig keine cdnas in GenBank zur Verfügung. Diese Tatsache erfordert, interne Exons, die in einer in silico Analyse leicht übersehen werden können, über das Exontrapping zu identifizieren. Im Gegensatz zum Exontrapping stellt die in silico Analyse, sofern die Sequenzen verfügbar sind, einen schnellen und einfachen Weg dar neue Gene einschließlich ihrer genomischen Struktur zu charakterisieren. In der 640 kb langen DNA-Sequenz, die im Rahmen dieser Arbeit mit Hilfe des Programmpakets NIX/HGMP untersucht wurden, konnten zwei nahezu vollständige Transkripte und vier EST-Cluster, bzw. einzelne EST-Klone gefunden werden, die Teil eines Transkripts sein können. Zusätzlich zu diesen potentiellen Transkripten wurden drei Pseudogene identifiziert. Die Anzahl der in silico gefundenen Transkripte auf gleicher Länge genomischer DNA ist vergleichbar mit der Anzahl der mit Hilfe des Exontrappings identifizierten Transkripte, die eine Homologie zu einem EST-Klon aufwiesen (vgl. Abbildung 18). Ein direkter Vergleich des Exontrappings mit der in silico Identifizierung von Transkripten in dieser Region kann allerdings erst nach Fertigstellung der Sequenzen der PAC- Klone, die für das Exontrapping verwendet wurden, gezogen werden. Auffällig sind aber dennoch Regionen höherer und niedrigerer Gendichte. Neben PAC-Klonen, auf die gleich mehrere Transkripte (1169J3, 85M6) zu liegen kommen, wurde in anderen Bereichen der genomischen DNA (entsprechend den PAC-Klonen 305G21 und 143A8) außer Sequenzhomologien zu einem Pseudogen (305G21) kein Transkript gefunden. In die Region der Länge von etwa 500 kb, in der die beiden PAC-Klone 305G21 und 143A8 zu liegen kommen, konnten bisher keine Gene kartiert werden. Bekannt ist auch die insgesamt ungleiche Verteilung der Gene auf die einzelnen Chromosomen. So sind beispielsweise auf Chromosom 1 oder 11 im Verhältnis mehr Gene zu finden als auf den Chromosomen 13 oder 18 (GenMap 98). Mögliche Funktionen der neuen Transkripte Für eine Beschreibung der im Rahmen dieser Arbeit identifizierten Transkripte wurden Expressionsanalysen auf Northern Blots und in verschiedenen Embryonalstadien der Maus durchgeführt. Durch den Nachweis der Expression kann das Vorliegen eines Artefakts bei der Durchführung des Exontrappings ausgeschlossen werden. Expressionsmuster geben zudem erste Hinweise, ob ein Gen in bestimmten Organen oder Embryonalstadien eine besondere Rolle spielt. Eine Vermutung über die Funktion der identifizierten Transkripte kann mit Hilfe von Ähnlichkeiten zu bekannten Genen getroffen werden. Für zwei der hier neu identifizierten Transkripte kann über die
5 Diskussion 66 Homologie zu einem bekannten Gen eine potentielle Funktion des abgelesenen Proteins hergeleitet werden. Eines dieser beiden Transkripte zeigt auf Proteinebene Ähnlichkeiten zwischen % zu einem Transkript, das aus Achlya ambisexualis isoliert wurde. Auf Northern Blots mit RNA aus Achlya ambisexualis konnte ein Produkt der Größe zwischen 3 und 4 kb detektiert werden (Schowalter, Toft und Sommer 1990). Mit cdna-proben aus der Maus (558312) und dem Menschen (588263) konnte im Northern Blot ein Transkriptionsprodukt ähnlicher Größe (4,3 und 4,4 kb) in allen getesteten Geweben sowie auch im Mausembryo nachgewiesen werden, wodurch die auf Proteinebene gefundene Homologie zwischen den beiden Transkripten bekräftigt wird. Für das aus Achlya ambisexualis isolierte Transkript wird aufgrund der enthaltenen Zinkfingerdomänen eine Rolle als transkriptioneller Regulator postuliert, möglicherweise handelt es sich hierbei um einen Steroidrezeptor (Schowalter, Toft und Sommer 1990). Die Zinkfingerdomäne konnte im humanen Transkript bisher allerdings nicht nachgewiesen werden, was wahrscheinlich auf die nur unvollständige cdna-sequenz zurückzuführen war, die in silico ausgewertet werden konnte. Das zweite Transkript, dessen Funktion mit Hilfe von Datenbankvergleichen beschrieben werden kann, zeigt Homologien zu cca3. Dieses Gen wurde in einem Differential Display-Ansatz zwischen wachsenden und wachstumsinhibierten Zellen aus der Leberzelllinie 3Y1 isoliert (Hayashi et al. 1997b). Es wurde zusammen mit zwei anderen Vertretern dieser Gruppe (cca1 und cca2) in wachstumsinhibierten Zellen identifiziert. Da außerdem beobachtet wurde, daß die mrna- Konzentration in sich regenerierenden Leberzellen abfällt, wurde postuliert, daß das Gen eine Rolle bei der Suppression der Zellteilung spielt (Hayashi et al. 1997a). Für eine regulatorische Funktion sprechen auch die zwei unterschiedlichen Domänen die Ankyrin-Domänen und die BTB-Domäne -, die auf Proteinebene sowohl im cca3-gen als auch im menschlichem Homologen gefunden wurden. Das Transkriptionsprodukt des cca3-gens konnte im Northern Blot im Gehirn, in der Milz, der Leber, der Niere und im Hoden der Ratte nachgewiesen werden (Hayashi et al. 1997a). Anders als in der Ratte konnte mit der entsprechenden homologen cdna-probe ( ) im Northern Blot mit Poly- A + -RNA aus menschlichem Gewebe, darunter auch RNA aus Leber, Gehirn, Milz und Niere, kein Transkript nachgewiesen werden. Möglicherweise liegt beim menschlichen Transkript eine wesentlich niedrigere und daher schwer nachweisbare Genexpression vor als beim Gen in der Ratte. Eine ähnliche Funktion des Gens aus der Ratte und des menschlichen Transkripts kann also nur über Homologien in der Proteinsequenz postuliert werden. Insbesondere die BTB-Domäne, die in beiden Proteinen vorhanden ist, spricht für eine Regulation auf DNA-Ebene. Für Transkripte mit geringer Ähnlichkeit zu bekannten Proteinen muß eine Homologie auf dem experimentellen Weg aufgrund ähnlicher Funktionen oder ähnlichen Expressionsmustern bestätigt oder ausgeschlossen werden. Eines der neuen Transkripte besitzt eine Ähnlichkeit von nur % mit dem sogenannten testes specific protein der Maus (Mazarakis et al. 1991). Der Nachweis einer Homologie zum testes specific protein auf Expressionsebene konnte nicht geführt werden, da eine humane Gewebeprobe aus Hoden, mit der eine spezifische Expression des Transkripts für dieses Gewebe hätte gezeigt werden können, nicht zur Verfügung stand. Eine schwache Expression des neu identifizierten Transkripts konnte allerdings in verschiedenen anderen Geweben (Gehirn, Niere, Milz) nachgewiesen werden, das heißt, es liegt keine spezifische Expression für ein bestimmtes Gewebe vor. Da sich zudem auf dem Northern Blot die Größe (9,7 kb) des gefundenen Transkripts erheblich
6 Diskussion 67 von der des bei Mazarakis et al. (1991) beschriebenen Transkripts (2 und 3 kb) unterscheidet, ist es unwahrscheinlich, daß es sich hierbei um ein Homologes zum testis specific protein handelt. Alle anderen der neu identifizierten Transkripte zeigten keine Ähnlichkeiten zu bekannten Genen. Über den Nachweis der Expression entweder in adulten Geweben oder im Mausembryo konnte jedoch gezeigt werden, daß es sich hierbei tatsächlich um exprimierte Sequenzen handelt. Für die Exons 247B4 und 1001E10 wurde eine Genexpression im Embryo festgestellt. Dies läßt auf eine Rolle dieser Genprodukte in der Embryonalentwicklung vornehmlich in der Entwicklung von Gehirn und neuronalem Gewebe (247B4 und 1001E5) und den sich entwickelnden Knochen (1001E5) schließen. Vor allem für das Exon 1001E10 stehen überwiegend Sequenzen aus der nichtcodierenden Region des 3 -Endes zur Verfügung, mit denen aufgrund des fehlenden Selektionsdrucks die Übereinstimmung zu homologen Genen weitaus niedriger und daher leichter zu übersehen ist. Es besteht aber auch die Möglichkeit, daß es sich hierbei um Transkripte neuer Genfamilien handelt. Eine Aufklärung der Funktion dieser neuen Gene ist somit von besonderem, zukünftigem Interesse. Für diejenigen Transkripte, für die auf RNA-Ebene kein Transkriptionsprodukt gefunden werden konnte, kann zum einen eine sehr niedrige Expression der Transkripte für den fehlenden Nachweis verantwortlich gemacht werden. Zum anderen waren auf den verwendeten Northern Blots nicht alle Gewebe oder Embryonalstadien repräsentiert. Eine Expression in einem dieser fehlenden Gewebe oder Embryonalstadien konnte daher nicht mit Hilfe der Northern Blot-Analyse oder in situ Hybridisierung detektiert werden. Es kann aber auch die Möglichkeit nicht ausgeschlossen werden, daß die für die Expressionsstudien verwendeten cdna-klone genomische DNA enthielt und diese daher nicht für den Nachweis exprimierter Sequenzen geeignet waren. Ausblick Das Interesse an der Kartierung des Chromosoms 11p13 gründet auf der Beobachtung von Deletionen in Verbindung mit verschiedenen Krankheiten, worunter das WAGR-Syndrom sowie unterschiedliche Tumorerkrankungen fallen. Bisher konnten bereits krankheitsrelevante Gene wie das Tumorsupessorgen WT1 oder das für die Aniridie verantwortliche Gen PAX6 in die Region 11p13 kartiert werden. Weitere Gene, insbesondere die auf 11p13 postulierten Tumorsupressorgene, die zur Klärung der genetischen Zusammenhänge der beobachteten Tumorerkrankungen beitragen können, wurden bisher nicht beschrieben. Auf der Basis des erstellten PAC-Contigs konnte mit der Isolierung von Genen begonnen werden, die in der Region 11p13 lokalisiert sind. Zwei der hier identifizierten Transkripte weisen eine Ähnlichkeit mit Proteinen auf, für die die Funktion eines transkriptionellen Regulators angenommen wird. Tumorsupressorgene, wie beispielsweise das WT1-Gen, sind häufig an der Regulation der Transkription beteiligt. Es kann daher die Frage aufgeworfen werden, ob die hier identifizierten Gene mit den bei Tumorpatienten gefundenen Deletionen in Zusammenhang stehen, auch wenn anhand des Expressionsmusters bisher kein Hinweis für eine spezifische Expression in den betroffenen Organen gefunden wurde. Um diese Frage zu klären, sind weitere Analysen dieser Transkripte erforderlich. Eine vollständige Charakterisierung dieser sowie auch der übrigen im Rahmen dieser Arbeit neu identifizierten Transkripte eröffnet somit ein interessantes Feld zukünftiger Forschungsaufgaben. Darüber hinaus können mit Hilfe des PAC-Contigs durch Exontrapping oder cdna-selektion weitere neue Transkripte isoliert werden. Die vollständige
7 Diskussion 68 Sequenzierung der 4,5 Mb DNA-Sequenz des hier erstellten PAC-Contigs bietet zudem die Chance, alle Gene dieser Region einschließlich ihres genomischen Aufbaus zu lokalisieren und somit die pathogenetischen Zusammenhänge der Region 11p13 vollständig zu klären.
8
3 Ergebnisse. 3.1 Die Speckling-Domäne von Wt1 umfaßt die Aminosäuren
 3 Ergebnisse 3.1 Die Speckling-Domäne von Wt1 umfaßt die Aminosäuren 76-120 Die Existenz verschiedener Isoformen von WT1 ist unter anderem auf die Verwendung einer für die Aminosäuren KTS kodierenden alternativen
3 Ergebnisse 3.1 Die Speckling-Domäne von Wt1 umfaßt die Aminosäuren 76-120 Die Existenz verschiedener Isoformen von WT1 ist unter anderem auf die Verwendung einer für die Aminosäuren KTS kodierenden alternativen
Hypothetische Modelle
 Hypothetische Modelle Heutiges Paper Vorgehensweise: Screening nach neuen Mutanten mit neuen Phänotyp Neuer Phänotyp: CPD, NPA- Resistenz (CPD, NPA: Wachstumshemmung durch Inhibierung des Auxin- Transport
Hypothetische Modelle Heutiges Paper Vorgehensweise: Screening nach neuen Mutanten mit neuen Phänotyp Neuer Phänotyp: CPD, NPA- Resistenz (CPD, NPA: Wachstumshemmung durch Inhibierung des Auxin- Transport
Klonierung von S2P Rolle der M19-Zellen. POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel
 Klonierung von S2P Rolle der M19-Zellen POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel Inhalt 1. Was ist eine humane genomische DNA-Bank? 2. Unterschied zwischen cdna-bank und genomischer DNA-Bank?
Klonierung von S2P Rolle der M19-Zellen POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel Inhalt 1. Was ist eine humane genomische DNA-Bank? 2. Unterschied zwischen cdna-bank und genomischer DNA-Bank?
Manuelle. Extraktion. DNA Extraktionskits
 Manuelle Extraktion DNA Extraktionskits XpressDNATM Tissue / Cell Line Kit... Tissue / Cell Line Kit Extraktion reiner genomischer DNA aus tierischem Gewebe Tierische Gewebe sind eine wichtige Quelle von
Manuelle Extraktion DNA Extraktionskits XpressDNATM Tissue / Cell Line Kit... Tissue / Cell Line Kit Extraktion reiner genomischer DNA aus tierischem Gewebe Tierische Gewebe sind eine wichtige Quelle von
AlgoBio WS 16/17 Protein-DNA Interaktionen ChiP-Seq Datenanalyse. Annalisa Marsico
 AlgoBio WS 16/17 Protein-DNA Interaktionen ChiP-Seq Datenanalyse Annalisa Marsico 6.02.2017 Protein-DNA Interaktionen Häufig binden sich Proteine an DNA, um ihre biologische Funktion zu regulieren. Transkriptionsfaktoren
AlgoBio WS 16/17 Protein-DNA Interaktionen ChiP-Seq Datenanalyse Annalisa Marsico 6.02.2017 Protein-DNA Interaktionen Häufig binden sich Proteine an DNA, um ihre biologische Funktion zu regulieren. Transkriptionsfaktoren
Inhalt Genexpression Microarrays E-Northern
 Inhalt Genexpression Microarrays E-Northern Genexpression Übersicht Definition Proteinbiosynthese Ablauf Transkription Translation Transport Expressionskontrolle Genexpression: Definition Realisierung
Inhalt Genexpression Microarrays E-Northern Genexpression Übersicht Definition Proteinbiosynthese Ablauf Transkription Translation Transport Expressionskontrolle Genexpression: Definition Realisierung
3.2. Genetisches Kartieren im Medakafisch
 Ergebnisse 64 wurde kloniert, und > 90% der untersuchten Klone enthielten das λ-fragment. Da die restlichen analysierten Klone keinen +/- -Polymorphismus auf Amplikons der beiden Stämme aufwiesen, wurde
Ergebnisse 64 wurde kloniert, und > 90% der untersuchten Klone enthielten das λ-fragment. Da die restlichen analysierten Klone keinen +/- -Polymorphismus auf Amplikons der beiden Stämme aufwiesen, wurde
Identifikation von Krankheitsgenen
 Identifikation von Krankheitsgenen bei monogenen Erkrankungen Definition eines Kandidatengens Mutationsanalyse von genomischer- oder cdna bei miteinander nicht verwandten Patienten Identifikation der,
Identifikation von Krankheitsgenen bei monogenen Erkrankungen Definition eines Kandidatengens Mutationsanalyse von genomischer- oder cdna bei miteinander nicht verwandten Patienten Identifikation der,
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr
 Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
Klausur zum Modul Molekularbiologie ILS, SS 2010 Freitag 6. August 10:00 Uhr Name: Matrikel-Nr.: Code Nummer: Bitte geben Sie Ihre Matrikel-Nr. und Ihren Namen an. Die Code-Nummer erhalten Sie zu Beginn
Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR)
 PCR Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR) von Kary B. Mullis entwickelt (1985) eigentlich im Mai 1983 bei einer nächtlichen Autofahrt erstes erfolgreiches Experiment am 16.12.1983
PCR Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR) von Kary B. Mullis entwickelt (1985) eigentlich im Mai 1983 bei einer nächtlichen Autofahrt erstes erfolgreiches Experiment am 16.12.1983
Bei Einbeziehung von neun Allelen in den Vergleich ergibt sich eine Mutation in 38 Generationen (350:9); das entspricht ca. 770 Jahren.
 336 DNA Genealogie Das Muster genetischer Variationen im Erbgut einer Person - zu gleichen Teilen von Mutter und Vater ererbt - definiert seine genetische Identität unveränderlich. Neben seiner Identität
336 DNA Genealogie Das Muster genetischer Variationen im Erbgut einer Person - zu gleichen Teilen von Mutter und Vater ererbt - definiert seine genetische Identität unveränderlich. Neben seiner Identität
Praktikum der Molekulargenetik
 Ulrich Kück (Hrsg.) Praktikum der Molekulargenetik unter der Mitarbeit von A. Bunse, H. Holländer-Czytko, S. Jeske, C. Klämbt, R. Klapper, I. Kubigsteltig, F. Meinhardt, J. Nickelsen, M. Nowrousian, S.
Ulrich Kück (Hrsg.) Praktikum der Molekulargenetik unter der Mitarbeit von A. Bunse, H. Holländer-Czytko, S. Jeske, C. Klämbt, R. Klapper, I. Kubigsteltig, F. Meinhardt, J. Nickelsen, M. Nowrousian, S.
Kaninchen: 1 cagattgaggagagcaccaccatcgtcacctcgcagttggcggaggtcagcgcagccgag 60
 Ergebnisse 6 3. Ergebnisse 3. Charakterisierung der zelllinienspezifischen cdn Die Entwicklung zweier Zelllinien, des epithelialen Trophoblasten und des pluripotenten Embryoblasten, ist der erste Differenzierungsschritt
Ergebnisse 6 3. Ergebnisse 3. Charakterisierung der zelllinienspezifischen cdn Die Entwicklung zweier Zelllinien, des epithelialen Trophoblasten und des pluripotenten Embryoblasten, ist der erste Differenzierungsschritt
Kulturen von humanen Nabelschnur-Endothelzellen (HUVEC) produzieren konstant Endothelin-1 (ET-1) und geben dieses in das Kulturmedium ab.
 4 ERGEBNISSE 4.1 Endothelin Kulturen von humanen Nabelschnur-Endothelzellen (HUVEC) produzieren konstant Endothelin-1 (ET-1) und geben dieses in das Kulturmedium ab. 4.1.1 Dosisabhängige Herabregulation
4 ERGEBNISSE 4.1 Endothelin Kulturen von humanen Nabelschnur-Endothelzellen (HUVEC) produzieren konstant Endothelin-1 (ET-1) und geben dieses in das Kulturmedium ab. 4.1.1 Dosisabhängige Herabregulation
Gentechnische Methoden
 Desmond S. T. Nicholl Gentechnische Methoden 2. Auflage Aus dem Englischen übersetzt von Renate FitzRoy und Kurt Beginnen Spektrum Akademischer Verlag Heidelberg Berlin Inhalt Vorwort XI 1. 1.1 1.2 1.3
Desmond S. T. Nicholl Gentechnische Methoden 2. Auflage Aus dem Englischen übersetzt von Renate FitzRoy und Kurt Beginnen Spektrum Akademischer Verlag Heidelberg Berlin Inhalt Vorwort XI 1. 1.1 1.2 1.3
Molekulare Genetik und Zellbiologie. Versuch 5 Präparation und Amplifikation menschlicher DNA. DNA Fingerprint VNTR-Analyse
 Molekulare Genetik und Zellbiologie Versuch 5 Präparation und Amplifikation menschlicher DNA DNA Fingerprint VNTR-Analyse Menschliche Genom 3000 Mb Gene und Gen-verwandte Sequenzen 900 Mb (30%) Extragene
Molekulare Genetik und Zellbiologie Versuch 5 Präparation und Amplifikation menschlicher DNA DNA Fingerprint VNTR-Analyse Menschliche Genom 3000 Mb Gene und Gen-verwandte Sequenzen 900 Mb (30%) Extragene
Abbildungs- und Tabellenverzeichnis Abkürzungsverzeichnis Genbezeichnung. 1. Einleitung 1
 Abbildungs- und Tabellenverzeichnis Abkürzungsverzeichnis Genbezeichnung VI VIII X 1. Einleitung 1 1.1 Das Plastom 1 1.2 Transkription in Chloroplasten 4 1.2.1 Die plastidäre Transkriptionsmaschinerie
Abbildungs- und Tabellenverzeichnis Abkürzungsverzeichnis Genbezeichnung VI VIII X 1. Einleitung 1 1.1 Das Plastom 1 1.2 Transkription in Chloroplasten 4 1.2.1 Die plastidäre Transkriptionsmaschinerie
BCDS - Biochemische Datenbanken und Software
 BCDS - Biochemische Datenbanken und Software Seminarinhalte Bioinformatische Genom- und Proteomanalyse Literaturrecherche und Zitation Naturwissenschaftliche Software Termine 25. Mai, 1. Juni, 8. Juni,
BCDS - Biochemische Datenbanken und Software Seminarinhalte Bioinformatische Genom- und Proteomanalyse Literaturrecherche und Zitation Naturwissenschaftliche Software Termine 25. Mai, 1. Juni, 8. Juni,
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 7 (11.07-15.07.) Methoden und Techniken II 1. Sie bekommen
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 7 (11.07-15.07.) Methoden und Techniken II 1. Sie bekommen
1 Einleitung Geschichte der DNase I DNase I: Proteinstruktur und Isoformen DNase I: Biochemische Eigenschaften 6
 Inhaltsverzeichnis 1 Einleitung 1 1.1 Geschichte der DNase I 2 1.2 DNase I: Proteinstruktur und Isoformen 4 1.3 DNase I: Biochemische Eigenschaften 6 1.4 DNase I-Genfamilie 8 1.4.1 DNase γ (DNase Y/ DNAS1L3/
Inhaltsverzeichnis 1 Einleitung 1 1.1 Geschichte der DNase I 2 1.2 DNase I: Proteinstruktur und Isoformen 4 1.3 DNase I: Biochemische Eigenschaften 6 1.4 DNase I-Genfamilie 8 1.4.1 DNase γ (DNase Y/ DNAS1L3/
Identifikation einer neuen WRKY-Transkriptionsfaktorbindungsstelle. in bioinformatisch identifizierten,
 Identifikation einer neuen WRKY-Transkriptionsfaktorbindungsstelle in bioinformatisch identifizierten, Pathogen-responsiven c/s-elementen aus Arabidopsis thaliana Von der Fakultät für Lebenswissenschaften
Identifikation einer neuen WRKY-Transkriptionsfaktorbindungsstelle in bioinformatisch identifizierten, Pathogen-responsiven c/s-elementen aus Arabidopsis thaliana Von der Fakultät für Lebenswissenschaften
2. Antisense-RNA als Regulationsprinzip der schweren Myosin- Kette (MyHC)
 7 2. Antisense-RNA als Regulationsprinzip der schweren Myosin- Kette (MyHC) In den ersten beiden Veröffentlichungen (2.1. und 2.2.) wurde die MyHC-Regulation im Myokard der Ratte analysiert. Untersuchungsgegenstand
7 2. Antisense-RNA als Regulationsprinzip der schweren Myosin- Kette (MyHC) In den ersten beiden Veröffentlichungen (2.1. und 2.2.) wurde die MyHC-Regulation im Myokard der Ratte analysiert. Untersuchungsgegenstand
Genetisch-epidemiologische Register-Studien
 Genetisch-epidemiologische Register-Studien am Beispiel des familiären Darmkrebses "HNPCC" (Teil 2) Dr. med. Christoph Engel Institut für Medizinische Informatik, Statistik und Epidemiologie (IMISE) Universität
Genetisch-epidemiologische Register-Studien am Beispiel des familiären Darmkrebses "HNPCC" (Teil 2) Dr. med. Christoph Engel Institut für Medizinische Informatik, Statistik und Epidemiologie (IMISE) Universität
Hämophilie Symposium, März , Reitter Sylvia
 Hämophilie Symposium, März 2010 FVIII-Gen liegt auf Xq28 (langer Arm des X-Chromosoms) x Hämophilie Erbgang I Hämophilie Erbgang II FVIII-Gen besteht aus 26 Exons mit 186 Kilobasenpaaren (kb); Exon 14
Hämophilie Symposium, März 2010 FVIII-Gen liegt auf Xq28 (langer Arm des X-Chromosoms) x Hämophilie Erbgang I Hämophilie Erbgang II FVIII-Gen besteht aus 26 Exons mit 186 Kilobasenpaaren (kb); Exon 14
Übung 11 Genregulation bei Prokaryoten
 Übung 11 Genregulation bei Prokaryoten Konzepte: Differentielle Genexpression Positive Genregulation Negative Genregulation cis-/trans-regulation 1. Auf welchen Ebenen kann Genregulation stattfinden? Definition
Übung 11 Genregulation bei Prokaryoten Konzepte: Differentielle Genexpression Positive Genregulation Negative Genregulation cis-/trans-regulation 1. Auf welchen Ebenen kann Genregulation stattfinden? Definition
Cornel Mülhardt. Molekularbiologie/ Genomics
 Cornel Mülhardt Molekularbiologie/ Genomics 1 Was ist denn Molekularbiologie", bitteschön? 1 1.1 Das Substrat der Molekularbiologie, oder : Molli-World für Anfänger 2 1.2 Was brauche ich zum Arbeiten?
Cornel Mülhardt Molekularbiologie/ Genomics 1 Was ist denn Molekularbiologie", bitteschön? 1 1.1 Das Substrat der Molekularbiologie, oder : Molli-World für Anfänger 2 1.2 Was brauche ich zum Arbeiten?
Genaktivierung und Genexpression
 Genaktivierung und Genexpression Unter Genexpression versteht man ganz allgemein die Ausprägung des Genotyps zum Phänotyp einer Zelle oder eines ganzen Organismus. Genotyp: Gesamtheit der Informationen
Genaktivierung und Genexpression Unter Genexpression versteht man ganz allgemein die Ausprägung des Genotyps zum Phänotyp einer Zelle oder eines ganzen Organismus. Genotyp: Gesamtheit der Informationen
Bestimmung des Schlüsselenzyms für den biologischen Abbau mittels der Planreal DNA-Methodik PRA-DNA
 Bestimmung des Schlüsselenzyms für den biologischen Abbau mittels der Planreal DNA-Methodik PRA-DNA Dr. Christoph Henkler, Planreal AG Der biologische Abbau von Schadstoffen erfolgt in den Zellen durch
Bestimmung des Schlüsselenzyms für den biologischen Abbau mittels der Planreal DNA-Methodik PRA-DNA Dr. Christoph Henkler, Planreal AG Der biologische Abbau von Schadstoffen erfolgt in den Zellen durch
4.1 Restriktionsenzymverdau von PCR-Produkten des β-catenin-gens
 4 Ergebnisse 4.1 Restriktionsenzymverdau von PR-Produkten des β-atenin-ens Für die Mutationsanalyse im Exon 3 des β-atenin-ens wurde in 19 Fällen die genomische DN aus umorgewebe untersucht, indem wie
4 Ergebnisse 4.1 Restriktionsenzymverdau von PR-Produkten des β-atenin-ens Für die Mutationsanalyse im Exon 3 des β-atenin-ens wurde in 19 Fällen die genomische DN aus umorgewebe untersucht, indem wie
Einleitung 3 1 ZUSAMMENFASSUNG
 Einleitung 3 1 ZUSAMMENFASSUNG In die Region p13 des menschlichen Chromosoms 11 kartieren mehrere krankheitsrelevante Gene wie das Wilms Tumor Gen WT1 oder das für die Aniridie verantwortliche Gen PAX6.
Einleitung 3 1 ZUSAMMENFASSUNG In die Region p13 des menschlichen Chromosoms 11 kartieren mehrere krankheitsrelevante Gene wie das Wilms Tumor Gen WT1 oder das für die Aniridie verantwortliche Gen PAX6.
Vorlesung Molekulare Humangenetik
 Vorlesung Molekulare Humangenetik WS 2013/2014 Dr. Shamsadin DNA-RNA-Protein Allgemeines Prüfungen o. Klausuren als indiv. Ergänzung 3LP benotet o. unbenotet Seminar Block 2LP Vorlesung Donnerstags 14-16
Vorlesung Molekulare Humangenetik WS 2013/2014 Dr. Shamsadin DNA-RNA-Protein Allgemeines Prüfungen o. Klausuren als indiv. Ergänzung 3LP benotet o. unbenotet Seminar Block 2LP Vorlesung Donnerstags 14-16
2.1 Die Entstehung des Gehirns aus neuralen Stammzellen Transkriptionsfaktoren in der Gehirnentwicklung...16
 Inhaltsverzeichnis Danksagung...3 Inhaltsverzeichnis...5 Abkürzungverzeichnis...1 1 Zielsetzung...4 2 Einleitung...6 2.1 Die Entstehung des Gehirns aus neuralen Stammzellen...6 2.2 Radiale Gliazellen...9
Inhaltsverzeichnis Danksagung...3 Inhaltsverzeichnis...5 Abkürzungverzeichnis...1 1 Zielsetzung...4 2 Einleitung...6 2.1 Die Entstehung des Gehirns aus neuralen Stammzellen...6 2.2 Radiale Gliazellen...9
C SB. Genomics Herausforderungen und Chancen. Genomics. Genomic data. Prinzipien dominieren über Detail-Fluten. in 10 Minuten!
 Genomics Herausforderungen und Chancen Prinzipien dominieren über Detail-Fluten Genomics in 10 Minuten! biol. Prin cip les Genomic data Dr.Thomas WERNER Scientific & Business Consulting +49 89 81889252
Genomics Herausforderungen und Chancen Prinzipien dominieren über Detail-Fluten Genomics in 10 Minuten! biol. Prin cip les Genomic data Dr.Thomas WERNER Scientific & Business Consulting +49 89 81889252
Untersuchungen zur differenziellen Genexpression im ZNS von Noradrenalintransporter-Knockout- und Wildtyp-Mäusen
 Untersuchungen zur differenziellen Genexpression im ZNS von Noradrenalintransporter-Knockout- und Wildtyp-Mäusen Inaugural-Dissertation zur Erlangung des Doktorgrades (Dr. rer. nat.) der Mathematisch-Naturwissenschaftlichen
Untersuchungen zur differenziellen Genexpression im ZNS von Noradrenalintransporter-Knockout- und Wildtyp-Mäusen Inaugural-Dissertation zur Erlangung des Doktorgrades (Dr. rer. nat.) der Mathematisch-Naturwissenschaftlichen
Molekulare Mechanismen der Signaltransduktion. 06 - Kartierung des AXR1 Gens + early auxin-induced genes Folien: http://tinyurl.
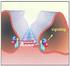 Molekulare Mechanismen der Signaltransduktion 06 - Kartierung des AXR1 Gens + early auxin-induced genes Folien: http://tinyurl.com/modul-mms bisheriges Modell auxin auxin AXR1 auxin response AXR1 potentieller
Molekulare Mechanismen der Signaltransduktion 06 - Kartierung des AXR1 Gens + early auxin-induced genes Folien: http://tinyurl.com/modul-mms bisheriges Modell auxin auxin AXR1 auxin response AXR1 potentieller
Interspergierte Repetitive Elemente
 Interspergierte Repetitive Elemente SINEs = short interspersed nuclear elements LINES = long interspersed nuclear elements MIR = mammalian wide interspersed repeats (Säugerspezifisch?) DNA-Transposons
Interspergierte Repetitive Elemente SINEs = short interspersed nuclear elements LINES = long interspersed nuclear elements MIR = mammalian wide interspersed repeats (Säugerspezifisch?) DNA-Transposons
Entwicklungs /gewebespezifische Genexpression
 Übung 11 Genregulation bei Prokaryoten Konzepte: Entwicklungs /gewebespezifische Genexpression Positive Genregulation Negative Genregulation cis /trans Regulation 1. Auf welchen Ebenen kann Genregulation
Übung 11 Genregulation bei Prokaryoten Konzepte: Entwicklungs /gewebespezifische Genexpression Positive Genregulation Negative Genregulation cis /trans Regulation 1. Auf welchen Ebenen kann Genregulation
Ergebnisse. I. Identifizierung intrazellulärer Interaktionspartner. Ergebnisse I. Identifizierung intrazellulärer Interaktionspartner
 Ergebnisse I. Identifizierung intrazellulärer Interaktionspartner Es sollten mithilfe des Yeast-Two-Hybrid-Systems Proteine identifiziert werden, die mit der zytoplasmatischen Domäne von CEACAM1-4L aus
Ergebnisse I. Identifizierung intrazellulärer Interaktionspartner Es sollten mithilfe des Yeast-Two-Hybrid-Systems Proteine identifiziert werden, die mit der zytoplasmatischen Domäne von CEACAM1-4L aus
3.2 Posttranslationelle Modifikation von Wt1 durch Phosphorylierung
 3.2 Posttranslationelle Modifikation von Wt1 durch Phosphorylierung Transkriptionsfaktoren erfahren oft eine posttranslationelle Modifikation in Form von Phosphorylierung und werden dadurch in ihrer Aktivität
3.2 Posttranslationelle Modifikation von Wt1 durch Phosphorylierung Transkriptionsfaktoren erfahren oft eine posttranslationelle Modifikation in Form von Phosphorylierung und werden dadurch in ihrer Aktivität
Transgene Organismen
 Transgene Organismen Themenübersicht 1) Einführung 2) Komplementäre DNA (cdna) 3) Vektoren 4) Einschleusung von Genen in Eukaryontenzellen 5) Ausmaß der Genexpression 6) Genausschaltung (Gen-Knockout)
Transgene Organismen Themenübersicht 1) Einführung 2) Komplementäre DNA (cdna) 3) Vektoren 4) Einschleusung von Genen in Eukaryontenzellen 5) Ausmaß der Genexpression 6) Genausschaltung (Gen-Knockout)
MODULE für den SCHULKOFFER GENTECHNIK
 MODULE für den SCHULKOFFER GENTECHNIK Modul 1 - DNA-Bastel-Set Zusammenbau eines Papiermodells in Form einer Doppelhelix sehr einfach, Unterstufe, ohne Koffer möglich Modul 2 - DNA-Isolierung aus Gemüse
MODULE für den SCHULKOFFER GENTECHNIK Modul 1 - DNA-Bastel-Set Zusammenbau eines Papiermodells in Form einer Doppelhelix sehr einfach, Unterstufe, ohne Koffer möglich Modul 2 - DNA-Isolierung aus Gemüse
Untersuchungen zur Funktion von Stärke-Synthasen in der Kartoffel (Solanum tuberosum L.)
 Untersuchungen zur Funktion von Stärke-Synthasen in der Kartoffel (Solanum tuberosum L.) Inaugural-Dissertation Erlangung der Doktorwürde im Fachbereich Biologie der Freien Univeisität Berlin vorgelegt
Untersuchungen zur Funktion von Stärke-Synthasen in der Kartoffel (Solanum tuberosum L.) Inaugural-Dissertation Erlangung der Doktorwürde im Fachbereich Biologie der Freien Univeisität Berlin vorgelegt
Dissertation. Zur Erlangung des akademischen Grades Doctor Rerum Naturalium ( Dr. rer. nat.) vorgelegt der
 Molekulare und funktionale Charakterisierung der neuronalen bhlh Transkritptionsfaktoren NSCL-1 und NSCL-2 Dissertation Zur Erlangung des akademischen Grades Doctor Rerum Naturalium ( Dr. rer. nat.) vorgelegt
Molekulare und funktionale Charakterisierung der neuronalen bhlh Transkritptionsfaktoren NSCL-1 und NSCL-2 Dissertation Zur Erlangung des akademischen Grades Doctor Rerum Naturalium ( Dr. rer. nat.) vorgelegt
Gentechnologie fur Einsteiger
 T. A. Brown Gentechnologie fur Einsteiger 6. Auflage ubersetzt von Sebastian Grundprinzipien der Klonierung und 1 1 Klonierung und DNA-Analyse so wichtig? 3 Friihe Entwicklungen in der Genetik 4 1.2 Die
T. A. Brown Gentechnologie fur Einsteiger 6. Auflage ubersetzt von Sebastian Grundprinzipien der Klonierung und 1 1 Klonierung und DNA-Analyse so wichtig? 3 Friihe Entwicklungen in der Genetik 4 1.2 Die
Multifunktionale DNA Kassetten zur konditionalen Mutagenese in der Maus
 Multifunktionale DNA Kassetten zur konditionalen Mutagenese in der Maus Von der Fakultat fur Lebenswissenschaften der Technischen Universitat Carolo-Wilhelmina zu Braunschweig zur Erlangung des Grades
Multifunktionale DNA Kassetten zur konditionalen Mutagenese in der Maus Von der Fakultat fur Lebenswissenschaften der Technischen Universitat Carolo-Wilhelmina zu Braunschweig zur Erlangung des Grades
Organisation und Evolution des Genoms
 Organisation und Evolution des Genoms Organisation und Evolution des Genoms Definition Genom: vollständige DNA-Sequenz eines Organismus I. Einfachstes Genom: Prokaryoten Zwei Gruppen, evolutionär unterschiedlicher
Organisation und Evolution des Genoms Organisation und Evolution des Genoms Definition Genom: vollständige DNA-Sequenz eines Organismus I. Einfachstes Genom: Prokaryoten Zwei Gruppen, evolutionär unterschiedlicher
Molekularbiologische Laboruntersuchungen. Labormedizinvorlesung Krisztina Káldi
 Molekularbiologische Laboruntersuchungen Labormedizinvorlesung 03.04.2017 Krisztina Káldi Ziel der molekularbiologischen Laboruntersuchungen Untersuchungen der DNA-Struktur und der Expression von RNA 3,2
Molekularbiologische Laboruntersuchungen Labormedizinvorlesung 03.04.2017 Krisztina Káldi Ziel der molekularbiologischen Laboruntersuchungen Untersuchungen der DNA-Struktur und der Expression von RNA 3,2
Methoden der Gentechnik
 Methoden der Gentechnik *** DNA-Rekombination und Klonierung *** 1. Allgemeine Grundprinzipien 1.1. Wesen der Gentechnik 1.2. Allgemeine Ziele der Gentechnik 1.3. Molekulare Voraussetzungen 1.4. Wichtige
Methoden der Gentechnik *** DNA-Rekombination und Klonierung *** 1. Allgemeine Grundprinzipien 1.1. Wesen der Gentechnik 1.2. Allgemeine Ziele der Gentechnik 1.3. Molekulare Voraussetzungen 1.4. Wichtige
Während der Synthese synthetisiert die Polymerase den neuen Strang in 5 3 Richtung und bewegt sich in 3 5 -Richtung am Matrizenstrang entlang:
 4.4 Replikation und PCR Ablauf der Replikation in vivo: Die Replikation wird von einer DNA-abhängigen DNA- Polymerase katalysiert. Jede DNA-Polymerase synthetisiert den neuen Strang in 5 3 Richtung, hierzu
4.4 Replikation und PCR Ablauf der Replikation in vivo: Die Replikation wird von einer DNA-abhängigen DNA- Polymerase katalysiert. Jede DNA-Polymerase synthetisiert den neuen Strang in 5 3 Richtung, hierzu
GEIM- TECHIMOLOGISCHE ARBEITSMETHODEN
 GEIM- TECHIMOLOGISCHE ARBEITSMETHODEN Ein Handbuch experimenteller Techniken und Verfahren Herausgegeben von Rudolf Hagemann Bearbeitet von Frank Baldauf, Jörn Belter, Sabine Brantl, Baimund Eck, Karsten
GEIM- TECHIMOLOGISCHE ARBEITSMETHODEN Ein Handbuch experimenteller Techniken und Verfahren Herausgegeben von Rudolf Hagemann Bearbeitet von Frank Baldauf, Jörn Belter, Sabine Brantl, Baimund Eck, Karsten
3.1 Altersabhängige Expression der AGE-Rezeptoren auf mrna und Proteinebene
 3 Ergebnisse 3.1 Altersabhängige Expression der AGE-Rezeptoren auf mrna und Proteinebene 3.1.1 Altersabhängige Genexpression der AGE-Rezeptoren Es wurde untersucht, ob es am menschlichen alternden Herzen
3 Ergebnisse 3.1 Altersabhängige Expression der AGE-Rezeptoren auf mrna und Proteinebene 3.1.1 Altersabhängige Genexpression der AGE-Rezeptoren Es wurde untersucht, ob es am menschlichen alternden Herzen
Algorithmen und Anwendungen zur Kartierung von Genomen
 Algorithmen und Anwendungen zur Kartierung von Genomen Dr. Dominik Grimm Probelehrveranstaltung Wissenschaftszentrum Straubing Hochschule Weihenstephan-Triesdorf Straubing, 14. Juli 2017 14. Juli 2017
Algorithmen und Anwendungen zur Kartierung von Genomen Dr. Dominik Grimm Probelehrveranstaltung Wissenschaftszentrum Straubing Hochschule Weihenstephan-Triesdorf Straubing, 14. Juli 2017 14. Juli 2017
Die RT-PCR Untersuchungen wurden anhand 27 Struma nodosa- (siehe Tab. 7) und 15 Adenom- (siehe Tab. 11) Präparaten durchgeführt.
 - 22-4 Ergebnisse 4.1 RT-PCR Die RT-PCR Untersuchungen wurden anhand 27 Struma nodosa- (siehe Tab. 7) und 15 Adenom- (siehe Tab. 11) Präparaten durchgeführt. 4.1.1 Struma nodosa Histologie Fas Fas CD 97
- 22-4 Ergebnisse 4.1 RT-PCR Die RT-PCR Untersuchungen wurden anhand 27 Struma nodosa- (siehe Tab. 7) und 15 Adenom- (siehe Tab. 11) Präparaten durchgeführt. 4.1.1 Struma nodosa Histologie Fas Fas CD 97
Hochdurchsatz Generierung und Analyse von Arabidopsis thaliana-proteinen
 MAX-PLANCK-INSTITUT FÜR MOLEKULARE GENETIK Hochdurchsatz Generierung und Analyse von Arabidopsis thaliana-proteinen Dissertation zur Erlangung der Doktorwürde des Fachbereichs Biologie, Chemie, Pharmazie
MAX-PLANCK-INSTITUT FÜR MOLEKULARE GENETIK Hochdurchsatz Generierung und Analyse von Arabidopsis thaliana-proteinen Dissertation zur Erlangung der Doktorwürde des Fachbereichs Biologie, Chemie, Pharmazie
Gentechnologie für Einsteiger
 T. A. Brown Gentechnologie für Einsteiger 3. Auflage Aus dem Englischen übersetzt von Sebastian Vogel Spektrum Akademischer Verlag Heidelberg Berlin Vorwort Vorwort zur dritten englischen Auflage Vorwort
T. A. Brown Gentechnologie für Einsteiger 3. Auflage Aus dem Englischen übersetzt von Sebastian Vogel Spektrum Akademischer Verlag Heidelberg Berlin Vorwort Vorwort zur dritten englischen Auflage Vorwort
Inhalt 1 Modellorganismen
 Inhalt 1 Modellorganismen....................................... 1 1.1 Escherichia coli....................................... 1 1.1.1 Historisches...................................... 3 1.1.2 Lebenszyklus.....................................
Inhalt 1 Modellorganismen....................................... 1 1.1 Escherichia coli....................................... 1 1.1.1 Historisches...................................... 3 1.1.2 Lebenszyklus.....................................
Projektskizze: Studie/ Auswertung/ Publikation
 Projektskizze: Studie/ Auswertung/ Publikation Name: PD Dr. Dr. Robert Bals, CAPNetz C11 Datum: 30. 8. 2007 Institution(en)/Autor(en): Klinikum der Universität Marburg Klinik für Innere Medizin mit Schwerpunkt
Projektskizze: Studie/ Auswertung/ Publikation Name: PD Dr. Dr. Robert Bals, CAPNetz C11 Datum: 30. 8. 2007 Institution(en)/Autor(en): Klinikum der Universität Marburg Klinik für Innere Medizin mit Schwerpunkt
Novartis Pharma AG Schullabor. Plasmid-DNA. Auf der Suche nach dem Antibiotikaresistenz Gen 2019 / 1
 Novartis Pharma AG Schullabor Plasmid-DNA Auf der Suche nach dem Antibiotikaresistenz Gen 019 / 1 Herausgeber Novartis Pharma AG, CH-00 Basel Kontaktadresse: Novartis Pharma AG Schullabor WKL-1..6A Postfach
Novartis Pharma AG Schullabor Plasmid-DNA Auf der Suche nach dem Antibiotikaresistenz Gen 019 / 1 Herausgeber Novartis Pharma AG, CH-00 Basel Kontaktadresse: Novartis Pharma AG Schullabor WKL-1..6A Postfach
C. R. Newton A. Graham 12'CR. 2. Auflage
 C. R. Newton A. Graham 12'CR 2. Auflage Vorwort 1 1 Danksagung 13 Abkürzungen 1 4 Teil 1 : Die wesentlichen Prinzipien und Methoden 1. Die Polymerasekettenreaktion (PCR) 19 1.1 Literatur 26 2. Geräte,
C. R. Newton A. Graham 12'CR 2. Auflage Vorwort 1 1 Danksagung 13 Abkürzungen 1 4 Teil 1 : Die wesentlichen Prinzipien und Methoden 1. Die Polymerasekettenreaktion (PCR) 19 1.1 Literatur 26 2. Geräte,
Entwicklungs /gewebespezifische Genexpression. Coexpression funktional überlappender Gene
 Übung 11 Genregulation bei Prokaryoten Konzepte: Entwicklungs /gewebespezifische Genexpression Coexpression funktional überlappender Gene Positive Genregulation Negative Genregulation cis /trans Regulation
Übung 11 Genregulation bei Prokaryoten Konzepte: Entwicklungs /gewebespezifische Genexpression Coexpression funktional überlappender Gene Positive Genregulation Negative Genregulation cis /trans Regulation
4. ERGEBNISSE. 4.2. Untersuchung des umgelagerten IgH Gens in Hodgkinzelllinien
 36 4. ERGEBNISSE 4.1. Immunglobulin Gentranskripte in Hodgkinzelllinien Mit Hilfe der RT PCR untersuchten wir die Expression umgelagerter Ig Gene in den Hodgkinzelllinien L1236, L428, L591 und KM-H2 sowie
36 4. ERGEBNISSE 4.1. Immunglobulin Gentranskripte in Hodgkinzelllinien Mit Hilfe der RT PCR untersuchten wir die Expression umgelagerter Ig Gene in den Hodgkinzelllinien L1236, L428, L591 und KM-H2 sowie
Anhang Anhang 8.1 Konstruktion transgener SQD1 -Pflanzen
 Anhang 92 8 Anhang 8.1 Konstruktion transgener SQD1-Pflanzen Mutagenese und ein dadurch entstehender Phänotyp eines Organismus kann Aufschluß über die Funktion eines betroffenen Gens geben. Die Erzeugung
Anhang 92 8 Anhang 8.1 Konstruktion transgener SQD1-Pflanzen Mutagenese und ein dadurch entstehender Phänotyp eines Organismus kann Aufschluß über die Funktion eines betroffenen Gens geben. Die Erzeugung
Kursinhalte der Weiterbildung Molekulare Biotechnologie (MNr.: 237 / 0411 / 2010)
 Kursinhalte der Weiterbildung Molekulare Biotechnologie (MNr.: 237 / 0411 / 2010) Schwerpunkte im Bereich BIOANALYTIK Polyacrylamidelektrophorese von Nukleinsäuren im Vertikalsystem Agarosegelelektrophorese
Kursinhalte der Weiterbildung Molekulare Biotechnologie (MNr.: 237 / 0411 / 2010) Schwerpunkte im Bereich BIOANALYTIK Polyacrylamidelektrophorese von Nukleinsäuren im Vertikalsystem Agarosegelelektrophorese
1.3 Begründe kurz, ob mit Hilfe der fünf in der vereinfachten ID-Card verwendeten Marker aus Aufgabe 1.1 das Geschlecht mit bestimmt werden kann.
 Übungsaufgaben zum DNA-Fingerprinter 1/6 1. In der EU wird die Einführung einer ID-Card (Nachfolger des Personalausweises, Entwurf s. Abb. 1) diskutiert, die neben Foto, äußeren Merkmalen und Fingerabdruck
Übungsaufgaben zum DNA-Fingerprinter 1/6 1. In der EU wird die Einführung einer ID-Card (Nachfolger des Personalausweises, Entwurf s. Abb. 1) diskutiert, die neben Foto, äußeren Merkmalen und Fingerabdruck
Antibiotika sind oft Inhibitoren der Genexpression
 Antibiotika sind oft Inhibitoren der Genexpression Inhibitoren der Transkription: Rifampicin, Actinomycin α-amanitin Inhibitoren der Translation: Puromycin, Streptomycin, Tetracycline, Chloramphenicol
Antibiotika sind oft Inhibitoren der Genexpression Inhibitoren der Transkription: Rifampicin, Actinomycin α-amanitin Inhibitoren der Translation: Puromycin, Streptomycin, Tetracycline, Chloramphenicol
Institut für Biochemie und Molekulare Medizin. Lecture 1 Translational components. Michael Altmann FS 2011
 Institut für Biochemie und Molekulare Medizin Lecture 1 Translational components Michael Altmann FS 2011 Gene Expression Fliessdiagramm der eukaryotischen Genexpression Die Expression eines Gens kann auf
Institut für Biochemie und Molekulare Medizin Lecture 1 Translational components Michael Altmann FS 2011 Gene Expression Fliessdiagramm der eukaryotischen Genexpression Die Expression eines Gens kann auf
3.1 Ergebnisse des endoskopischen Screenings. Im Zeitraum von Mai 2000 bis August 2001 wurde bei insgesamt 148 Kopf-Hals-
 32 3. Ergebnisse 3.1 Ergebnisse des endoskopischen Screenings Im Zeitraum von Mai 2000 bis August 2001 wurde bei insgesamt 148 Kopf-Hals- Tumorpatienten eine einmalige Videoösophagoskopie mit routinemäßigen
32 3. Ergebnisse 3.1 Ergebnisse des endoskopischen Screenings Im Zeitraum von Mai 2000 bis August 2001 wurde bei insgesamt 148 Kopf-Hals- Tumorpatienten eine einmalige Videoösophagoskopie mit routinemäßigen
Wirkungen auf die Blut-Hirn-Schranke, DNA-Schädigung
 Wirkungen auf die Blut-Hirn-Schranke, DNA-Schädigung Dr. Monika Asmuß Bundesamt für Strahlenschutz Mobilfunk und Gesundheit BfS-Informationsveranstaltung, 25. Juni 2009, München 1 Blut-Hirn-Schranke (BHS)
Wirkungen auf die Blut-Hirn-Schranke, DNA-Schädigung Dr. Monika Asmuß Bundesamt für Strahlenschutz Mobilfunk und Gesundheit BfS-Informationsveranstaltung, 25. Juni 2009, München 1 Blut-Hirn-Schranke (BHS)
Charakterisierung der mirna-expression im großzellig anaplastischen T-Zell-Lymphom
 Charakterisierung der mirna-expression im großzellig anaplastischen T-Zell-Lymphom Dissertation der Mathematisch-Naturwissenschaftlichen Fakultät der Eberhard Karls Universität Tübingen zur Erlangung des
Charakterisierung der mirna-expression im großzellig anaplastischen T-Zell-Lymphom Dissertation der Mathematisch-Naturwissenschaftlichen Fakultät der Eberhard Karls Universität Tübingen zur Erlangung des
Die gewebespezifische Genexpression in der Epidermis des Gerstenblattes
 Die gewebespezifische Genexpression in der Epidermis des Gerstenblattes Dissertation zur Erlangung des naturwissenschaftlichen Doktorgrades der Bayerischen Julius-Maximilians-Universität Würzburg vorgelegt
Die gewebespezifische Genexpression in der Epidermis des Gerstenblattes Dissertation zur Erlangung des naturwissenschaftlichen Doktorgrades der Bayerischen Julius-Maximilians-Universität Würzburg vorgelegt
Genexpressionsdatenbanken
 Genexpressionsdatenbanken ArrayExpress Gliederung Mikroarrays Struktur von Genexpressionsdatenbanken Arrayexpress Aufbau und Statistik Standardisierung Abfragen und Einstellen von Daten Mikroarrays Glasplatte
Genexpressionsdatenbanken ArrayExpress Gliederung Mikroarrays Struktur von Genexpressionsdatenbanken Arrayexpress Aufbau und Statistik Standardisierung Abfragen und Einstellen von Daten Mikroarrays Glasplatte
Influenzaüberwachung bei Mensch und Schwein Oktober 2009 Dezember 2015
 März 2016 Influenzaüberwachung bei Mensch und Schwein Oktober 2009 Dezember 2015 Hintergrund: 2009 löste das Influenza A(H1N1)pdm09 Virus eine weltweite Pandemie aus. Die Sequenzierung des Virus ergab,
März 2016 Influenzaüberwachung bei Mensch und Schwein Oktober 2009 Dezember 2015 Hintergrund: 2009 löste das Influenza A(H1N1)pdm09 Virus eine weltweite Pandemie aus. Die Sequenzierung des Virus ergab,
Vortrag von Philipp Nerke und Bruno Voigt
 Vortrag von Philipp Nerke und Bruno Voigt Was war bekannt? Wirkung von Auxin Streckungswachstum Apicaldominanz Gravitropismus Laterales Wurzelwachstum Bekannte Gene der Auxin-Regulation AXR1 AXR4 AUX1
Vortrag von Philipp Nerke und Bruno Voigt Was war bekannt? Wirkung von Auxin Streckungswachstum Apicaldominanz Gravitropismus Laterales Wurzelwachstum Bekannte Gene der Auxin-Regulation AXR1 AXR4 AUX1
III. Ergebnisteil CD8 CD4. III.1. Separation von CD4 + und CD8 + T-Lymphozyten aus peripherem Blut
 27 III. Ergebnisteil III.1. Separation von CD4 + und CD8 + T-Lymphozyten aus peripherem Blut Durch Anwendung des vorher schon im Material- und Methodenteil beschriebenen MACS-Systems konnten CD4 + bzw.
27 III. Ergebnisteil III.1. Separation von CD4 + und CD8 + T-Lymphozyten aus peripherem Blut Durch Anwendung des vorher schon im Material- und Methodenteil beschriebenen MACS-Systems konnten CD4 + bzw.
Kerstin Brachhold (Autor) Das Basalapparat-Subproteom von Chlamydomonas reinhardtii
 Kerstin Brachhold (Autor) Das Basalapparat-Subproteom von Chlamydomonas reinhardtii https://cuvillier.de/de/shop/publications/1867 Copyright: Cuvillier Verlag, Inhaberin Annette Jentzsch-Cuvillier, Nonnenstieg
Kerstin Brachhold (Autor) Das Basalapparat-Subproteom von Chlamydomonas reinhardtii https://cuvillier.de/de/shop/publications/1867 Copyright: Cuvillier Verlag, Inhaberin Annette Jentzsch-Cuvillier, Nonnenstieg
Personalisierte Medizin
 Personalisierte Medizin Möglichkeiten und Grenzen Prof. Dr. Friedemann Horn Universität Leipzig, Institut für Klinische Immunologie, Molekulare Immunologie Fraunhofer Institut für Zelltherapie und Immunologie
Personalisierte Medizin Möglichkeiten und Grenzen Prof. Dr. Friedemann Horn Universität Leipzig, Institut für Klinische Immunologie, Molekulare Immunologie Fraunhofer Institut für Zelltherapie und Immunologie
Posttranskriptionale Veränderungen der Genexpression bei hereditären Erkrankungen
 Posttranskriptionale Veränderungen der Genexpression bei hereditären Erkrankungen Dissertation zur Erlangung des Doktorgrades Dr. rer. nat. des Fachbereichs Biologie, Chemie, Pharmazie der Freien Universität
Posttranskriptionale Veränderungen der Genexpression bei hereditären Erkrankungen Dissertation zur Erlangung des Doktorgrades Dr. rer. nat. des Fachbereichs Biologie, Chemie, Pharmazie der Freien Universität
MRSA Typisierungen
 EUREGIO Gronau/Enschede MRSA Typisierungen 2012-2013 Ansprechpartner Dr. med. R. Köck Institut für Hygiene Universitätsklinikum Münster robin.koeck@ukmuenster.de Tel. 0251-83-55348 0 Inhaltsverzeichnis
EUREGIO Gronau/Enschede MRSA Typisierungen 2012-2013 Ansprechpartner Dr. med. R. Köck Institut für Hygiene Universitätsklinikum Münster robin.koeck@ukmuenster.de Tel. 0251-83-55348 0 Inhaltsverzeichnis
5 Diskussion und Ausblick
 5 Diskussion und Ausblick Für biochemischen Untersuchungen wie das Testen potentieller inhibitorischer Substanzen oder Strukturuntersuchungen durch Proteinkristallisation oder NMR-Spektroskopie, aber auch
5 Diskussion und Ausblick Für biochemischen Untersuchungen wie das Testen potentieller inhibitorischer Substanzen oder Strukturuntersuchungen durch Proteinkristallisation oder NMR-Spektroskopie, aber auch
Genetik Praktikumsklausur SS2005
 Genetik Praktikumsklausur SS2005 1. Aufgabe: Der Genotyp AbaB wird geselbstet, dabei werden 256 Nachkommen gebildet. Davon erhalten 16 Pflanzen den Genotyp ABAB a) gekoppelt b) nicht gekoppelt c) teilweise
Genetik Praktikumsklausur SS2005 1. Aufgabe: Der Genotyp AbaB wird geselbstet, dabei werden 256 Nachkommen gebildet. Davon erhalten 16 Pflanzen den Genotyp ABAB a) gekoppelt b) nicht gekoppelt c) teilweise
Herstellung einer Deletion und interne Sequenzierung des Klons DA 10.2
 Herstellung einer Deletion und interne Sequenzierung des Klons DA 10.2 Betreuung durch Dr. I. Haussmann und Zusammenarbeit mit S. Bantle und D. Auerbach Institut für Zellbiologie, ETH Zürich 1. Zusammenfassung:
Herstellung einer Deletion und interne Sequenzierung des Klons DA 10.2 Betreuung durch Dr. I. Haussmann und Zusammenarbeit mit S. Bantle und D. Auerbach Institut für Zellbiologie, ETH Zürich 1. Zusammenfassung:
VORANGEGANGENE MODELLE
 VORANGEGANGENE MODELLE UNSER THEMA HEUTE Ziel dieses Papers: - Nähere Charakterisierung der AuxREs - Analyse eines zu den AuxREs gehörenden Transkriptionsfaktors WAS BEREITS BEKANNT WAR: - Auxin moduliert
VORANGEGANGENE MODELLE UNSER THEMA HEUTE Ziel dieses Papers: - Nähere Charakterisierung der AuxREs - Analyse eines zu den AuxREs gehörenden Transkriptionsfaktors WAS BEREITS BEKANNT WAR: - Auxin moduliert
27 Funktionelle Genomanalysen Sachverzeichnis
 Inhaltsverzeichnis 27 Funktionelle Genomanalysen... 543 27.1 Einleitung... 543 27.2 RNA-Interferenz: sirna/shrna-screens 543 Gunter Meister 27.3 Knock-out-Technologie: homologe Rekombination im Genom der
Inhaltsverzeichnis 27 Funktionelle Genomanalysen... 543 27.1 Einleitung... 543 27.2 RNA-Interferenz: sirna/shrna-screens 543 Gunter Meister 27.3 Knock-out-Technologie: homologe Rekombination im Genom der
Neue Enzyme für ein altes Organeil: Kryptische peroxisomale Lokalisationssignale in Pilzen. Dissertation
 Neue Enzyme für ein altes Organeil: Kryptische peroxisomale Lokalisationssignale in Pilzen Dissertation zur Erlangung des Doktorgrades der Naturwissenschaften (Dr. rer. nat.) Dem Fachbereich Biologie der
Neue Enzyme für ein altes Organeil: Kryptische peroxisomale Lokalisationssignale in Pilzen Dissertation zur Erlangung des Doktorgrades der Naturwissenschaften (Dr. rer. nat.) Dem Fachbereich Biologie der
Sequenzierung und Charakterisierung der Triosephosphat-Isomerase aus Tenebrio molitor (Mehlwurm)
 Naturwissenschaft Daniel Knobeloch Sequenzierung und Charakterisierung der Triosephosphat-Isomerase aus Tenebrio molitor (Mehlwurm) Diplomarbeit Bibliografische Information der Deutschen Nationalbibliothek:
Naturwissenschaft Daniel Knobeloch Sequenzierung und Charakterisierung der Triosephosphat-Isomerase aus Tenebrio molitor (Mehlwurm) Diplomarbeit Bibliografische Information der Deutschen Nationalbibliothek:
Bioinformatik II: Phylogenetik
 Bioinformatik II: Phylogenetik phylogenetisch Phylai: griechische Klans phylum: der Stamm phylogenetisch: die Stammesgeschichte von Lebewesen betreffend Hierarchien der Klassifikation: Domäne: Eukaryonten
Bioinformatik II: Phylogenetik phylogenetisch Phylai: griechische Klans phylum: der Stamm phylogenetisch: die Stammesgeschichte von Lebewesen betreffend Hierarchien der Klassifikation: Domäne: Eukaryonten
Berichte aus der Medizin. Bernd Rautenstrauß
 Berichte aus der Medizin Bernd Rautenstrauß Hereditäre motorische und sensible Neuropathien: Experimentelle Beiträge zur Charakterisierung der ursächlichen Mutationen und ihrer phänotypischen Auswirkungen.
Berichte aus der Medizin Bernd Rautenstrauß Hereditäre motorische und sensible Neuropathien: Experimentelle Beiträge zur Charakterisierung der ursächlichen Mutationen und ihrer phänotypischen Auswirkungen.
https://cuvillier.de/de/shop/publications/4021
 Jürgen Henrich (Autor) Erstellung segmentspezifischer molekularer Marker mittels Mikrodissektion und physikalische Kartierung der Resistenz gegen Schadinsekten (Diatraea spp.) bei tropischem Mais (Zea
Jürgen Henrich (Autor) Erstellung segmentspezifischer molekularer Marker mittels Mikrodissektion und physikalische Kartierung der Resistenz gegen Schadinsekten (Diatraea spp.) bei tropischem Mais (Zea
Molekularbiologische Datenbanken
 Molekularbiologische Datenbanken Übungen Aufgabe 2 Silke Trißl Ulf Leser Wissensmanagement in der Bioinformatik Microarray oder Expressionsanalyse Gleiche Erbinformation in der Zelle (Genom), aber viele
Molekularbiologische Datenbanken Übungen Aufgabe 2 Silke Trißl Ulf Leser Wissensmanagement in der Bioinformatik Microarray oder Expressionsanalyse Gleiche Erbinformation in der Zelle (Genom), aber viele
Zusätzliche Behandlungs möglichkeiten für Ihre Patienten
 Zusätzliche Behandlungs möglichkeiten für Ihre Patienten Über FoundationOne Bei dem validierten umfassenden Tumorprofil von FoundationOne wird die gesamte codierende Sequenz von 315 krebsassoziierten Genen
Zusätzliche Behandlungs möglichkeiten für Ihre Patienten Über FoundationOne Bei dem validierten umfassenden Tumorprofil von FoundationOne wird die gesamte codierende Sequenz von 315 krebsassoziierten Genen
Typ eines Gens oder jede Abweichung der DNA-Sequenz eines Gens. Heterozygot verschiedene Allele in der Zygote (= diploide Zelle)
 Die Klausur besteht aus insgesamt 11 Seiten (1 Deckblatt + 10 Seiten). Bitte geben Sie auf jeder Seite Ihren Namen oben rechts an. Bei der Korrektur können nur solche Seiten berücksichtigt werden, die
Die Klausur besteht aus insgesamt 11 Seiten (1 Deckblatt + 10 Seiten). Bitte geben Sie auf jeder Seite Ihren Namen oben rechts an. Bei der Korrektur können nur solche Seiten berücksichtigt werden, die
KV: Genexpression und Transkription Michael Altmann
 Institut für Biochemie und Molekulare Medizin KV: Genexpression und Transkription Michael Altmann Herbstsemester 2008/2009 Übersicht VL Genexpression / Transkription 1.) Was ist ein Gen? 2.) Welche Arten
Institut für Biochemie und Molekulare Medizin KV: Genexpression und Transkription Michael Altmann Herbstsemester 2008/2009 Übersicht VL Genexpression / Transkription 1.) Was ist ein Gen? 2.) Welche Arten
Eline Biedermann (Autor) Untersuchungen zur Charakterisierung von Prenyltransferasen aus Hypericum-Arten nach Expression in Nicotiana benthamiana
 Eline Biedermann (Autor) Untersuchungen zur Charakterisierung von Prenyltransferasen aus Hypericum-Arten nach Expression in Nicotiana benthamiana https://cuvillier.de/de/shop/publications/7653 Copyright:
Eline Biedermann (Autor) Untersuchungen zur Charakterisierung von Prenyltransferasen aus Hypericum-Arten nach Expression in Nicotiana benthamiana https://cuvillier.de/de/shop/publications/7653 Copyright:
Arten der Intronen. Spliceosome Struktur des snrnp U1. Spliceosome. Vorlesung 3: Evolution des eukaryotischen Genoms 4/20/11
 Vorlesung 3: Evolution des eukaryotischen Genoms Struktur des eukaryotischen Gens Intronen und Exonen Genduplikation--Familien des Gens Eiweißdomänen (Protein domains) Domänen und Exonen: sind sie verwandt?
Vorlesung 3: Evolution des eukaryotischen Genoms Struktur des eukaryotischen Gens Intronen und Exonen Genduplikation--Familien des Gens Eiweißdomänen (Protein domains) Domänen und Exonen: sind sie verwandt?
Stammzüchtung. Selektion von natürlichen Varianten. Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese
 Stammzüchtung Selektion von natürlichen Varianten Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese Kreuzungen genetische Rekombination Sexuelle Kreuzungen Induzierte Zellfusion
Stammzüchtung Selektion von natürlichen Varianten Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese Kreuzungen genetische Rekombination Sexuelle Kreuzungen Induzierte Zellfusion
AUFGABENSAMMLUNG. Restriktionsenzyme. Füllen Sie den Lückentext aus. Gentechnik Schroedel, Braunschweig
 Restriktionsenzyme Füllen Sie den Lückentext aus. PCR 1a Mit dem folgenden Quiz können Sie Ihr Wissen zum Thema PCR überprüfen. Klicken Sie jeweils die richtige Antwort an. PCR 1b Mit dem folgenden Quiz
Restriktionsenzyme Füllen Sie den Lückentext aus. PCR 1a Mit dem folgenden Quiz können Sie Ihr Wissen zum Thema PCR überprüfen. Klicken Sie jeweils die richtige Antwort an. PCR 1b Mit dem folgenden Quiz
Ubiquitin-vermittelte Cadmium-Resistenz und MAC 1-abhängige Regulation des Kupferund Eisenstoffwechsels
 0 Molekulargenetische Analyse Metall-abhängiger Prozesse in S. cerevisiae: Ubiquitin-vermittelte Cadmium-Resistenz und MAC 1-abhängige Regulation des Kupferund Eisenstoffwechsels DISSERTATION der Fakultät
0 Molekulargenetische Analyse Metall-abhängiger Prozesse in S. cerevisiae: Ubiquitin-vermittelte Cadmium-Resistenz und MAC 1-abhängige Regulation des Kupferund Eisenstoffwechsels DISSERTATION der Fakultät
