Vorläufige Patentanmeldung. Entwicklung eines Nukleinsäurepools zum Nachweis aller bisher bekannten humanen Papillomviren
|
|
|
- Heidi Breiner
- vor 6 Jahren
- Abrufe
Transkript
1 Dr. Bernd Zorr Fichtestraße Berlin Deutschland Tel Tel Vorläufige Patentanmeldung Entwicklung eines Nukleinsäurepools zum Nachweis aller bisher bekannten humanen Papillomviren Applicant: : Dr. Bernd Zorr, Fichtestraße 34, 1096 Berlin, Deutschland Inventor: Dr. Bernd Zorr, Fichtestraße 34, 1096 Berlin, Deutschland Representative: : Dr. Bernd Zorr, Fichtestraße 34, 1096 Berlin, Deutschland Stand der Technik Durch die Verwendung molekularbiologischer Methoden ist es heute ein Leichtes, erregerspezifische Nukleinsäuren nachzuweisen. Kompliziert wird der Nachweis durch eine den Erregern inhärente Heterogenität im genetischen Material. Bei humanen Papillomviren- dem ätiologischen Agenz des Gebärmutterhalskrebses und anderer Tumoren- ist die Vielfalt besonders ausgeprägt. Verschiedene HPV Typen können verschiedene Krankheitsbilder induzieren. Der Nachweis einzelner HPV- Typen ist Stand der Technik.
2 Lösung der Aufgabe In einem Nachweisschritt alle HPV Typen auf molekularbiologischem Wege zu erfassen ist die zu lösende Aufgabe. Es wird ein Nukleinsäurepool beschrieben, in der Regel mit einer Länge von 38 Basen, der aus einem hoch konservierten Genomabschnitt, den alle humanen Papillomviren besitzen, durch Sequenzalignment bestimmt wurde. Der Nukleinsäurepool ist in dem Sinne eine Erfindung, da er im Gegensatz zu erregerspezifischen Sequenzen in der Natur nicht vorkommt. Die Herstellung dieser künstlichen Mischung führt zum Nachweis aller bisher natürlich vorkommender humanen Papillomviren. Der Nukleinsäurepool besitzt folgende Zusammensetzung: KGA RGA RTA TGA TTT RCA RTT YRT WTT TCA RYT RTG YA Die Bezeichnung degenerierter Nukleinsäurepositionen entspricht der internationalen Nomenklatur. Dieser Nukleinsäurepool kann am freien 5 oder 3 Ende mit weiteren Basen modifiziert werden. Beispiel Es wird im folgenden gezeigt, welche Sequenzen der Nukleinsäurepool aus einer Datenbank mit vielen irrelevanten Sequenzen findet. Der Nukleinsäurepool findet nur erregerspezifische Nukleinsäuren der humanen Papillomviren (HPV):
3 ! FINDPATTERNS on GeAll:* allowing 0 mismatches! 1 KGA RGA RTA TGA TTT RCA RTT YRT WTT TCA RYT RTG YA July 20, :08.. HSA ck: 3474 len: 8,039! Aj Homo sapiens partial N-myc (exon 3), HPV45 L2, HPV45 L1, HPV45 E6 4,897: CATGT GGAGGAATATGATTTACAGTTTATTTTTCAGTTGTGCA CTATT AF ck: 4448 len: 261! Af Human papillomavirus isolate HPVXS1 L1 protein gene, partial cds. 69: CACGG TGAGGAATATGATTTGCAATTTATATTTCAGTTGTGTA AAGTC AF ck: 8342 len: 7,904! Af Human papillomavirus type 16 isolate 16W12E, complete genome. 7/2 6,737: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA AR ck: 8394 len: 1,517! Ar Sequence 1 from patent US /1998 AR ck: 8012 len: 1,517! Ar Sequence 2 from patent US /1998 AR ck: 8394 len: 1,517! Ar Sequence 1 from patent US /1999 AR ck: 8012 len: 1,517! Ar Sequence 2 from patent US /1999 AR ck: 1586 len: 1,524! Ar Sequence 1 from patent US /1999 1,104: CATGT TGAAGAATATGATTTGCAGTTTATTTTTCAGTTATGTA CTATT
4 AR ck: 1586 len: 1,524! Ar Sequence 1 from patent US /1999 1,104: CATGT TGAAGAATATGATTTGCAGTTTATTTTTCAGTTATGTA CTATT I13522 ck: 8394 len: 1,517! I13522 Sequence 1 from patent US /1995 I13523 ck: 8012 len: 1,517! I13523 Sequence 2 from patent US /1995 I22532 ck: 8212 len: 415! I22532 Sequence 20 from patent US / : CATGT GGAGGAATATGATTTACAGTTTATTTTTCAGTTGTGCA CTATT I22791 ck: 2191 len: 394! I22791 Sequence 279 from patent US / : CATGT GGAGGAATATGATTTACAATTTATATTTCAATTGTGTA CTATC I22795 ck: 1731 len: 467! I22795 Sequence 283 from patent US / : CATGT TGAGGAATATGATTTGCAATTTATATTTCAGTTGTGTA CTATA I22796 ck: 6941 len: 464! I22796 Sequence 284 from patent US / : CATGG TGAAGAATATGATTTACAGTTTATTTTTCAGTTATGTA AAATA I22797 ck: 6731 len: 467! I22797 Sequence 285 from patent US / : CACGT GGAGGAGTATGATTTACAATTTATATTTCAACTGTGTA CTGTC I22800 ck: 1223 len: 467! I22800 Sequence 288 from patent US / : CATGT GGAGGAATATGATTTACAGTTTATTTTTCAGTTGTGCA CTATT
5 I22807 ck: 6991 len: 449! I22807 Sequence 295 from patent US / : CATAT GGAGGAATATGATTTGCAGTTCATTTTTCAACTGTGCA AAATA I47357 ck: 8212 len: 415! I47357 Sequence 20 from patent US / : CATGT GGAGGAATATGATTTACAGTTTATTTTTCAGTTGTGCA CTATT I47616 ck: 2191 len: 394! I47616 Sequence 279 from patent US / : CATGT GGAGGAATATGATTTACAATTTATATTTCAATTGTGTA CTATC I47620 ck: 1731 len: 467! I47620 Sequence 283 from patent US / : CATGT TGAGGAATATGATTTGCAATTTATATTTCAGTTGTGTA CTATA I47621 ck: 6941 len: 464! I47621 Sequence 284 from patent US / : CATGG TGAAGAATATGATTTACAGTTTATTTTTCAGTTATGTA AAATA I47622 ck: 6731 len: 467! I47622 Sequence 285 from patent US / : CACGT GGAGGAGTATGATTTACAATTTATATTTCAACTGTGTA CTGTC I47625 ck: 1223 len: 467! I47625 Sequence 288 from patent US / : CATGT GGAGGAATATGATTTACAGTTTATTTTTCAGTTGTGCA CTATT I47632 ck: 6991 len: 449! I47632 Sequence 295 from patent US / : CATAT GGAGGAATATGATTTGCAGTTCATTTTTCAACTGTGCA AAATA I60253 ck: 5647 len: 7,833! I60253 Sequence 9 from patent US /1997 6,743: CACGT GGAGGAGTATGATTTACAATTTATATTTCAACTGTGTA CTGTC I64482 ck: 5647 len: 7,833! I64482 Sequence 9 from patent US /1997
6 6,743: CACGT GGAGGAGTATGATTTACAATTTATATTTCAACTGTGTA CTGTC I70142 ck: 6074 len: 7,904! I70142 Sequence 1 from patent US /1998 6,737: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA I70143 ck: 5970 len: 7,904! I70143 Sequence 2 from patent US /1998 6,737: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA I72345 ck: 6074 len: 7,904! I72345 Sequence 1 from patent US /1998 6,737: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA I80878 ck: 8394 len: 1,517! I80878 Sequence 1 from patent US /1998 I80879 ck: 8012 len: 1,517! I80879 Sequence 2 from patent US /1998 HSA ck: 3474 len: 8,039! Aj Homo sapiens partial N-myc (exon 3), HPV45 L2, HPV45 L1, HPV45 E6 4,897: CATGT GGAGGAATATGATTTACAGTTTATTTTTCAGTTGTGCA CTATT AF ck: 559 len: 1,518! Af Human papillomavirus type 16 Sen32 late major capsid protein (L1) AF ck: 1053 len: 1,518! Af Human papillomavirus type 16 Phi1 late major capsid protein (L1) AF ck: 2446 len: 1,503! Af Human papillomavirus type 6 clinical biopsy F49413 major capsid p
7 AF ck: 2446 len: 1,503! Af Human papillomavirus type 6 clinical biopsy M48163 major capsid p AF ck: 2446 len: 1,503! Af Human papillomavirus type 6 clinical biopsy M33382 major capsid p AF ck: 2298 len: 1,503! Af Human papillomavirus type 6 clinical biopsy F47718 major capsid p AF ck: 2298 len: 1,503! Af Human papillomavirus type 6 clinical biopsy M39010 major capsid p AF ck: 2298 len: 1,503! Af Human papillomavirus type 6 clinical biopsy M47769 major capsid p AF ck: 2298 len: 1,503! Af Human papillomavirus type 6 clinical biopsy M49576 major capsid p AF ck: 1171 len: 1,503! Af Human papillomavirus type 6 clinical biopsy M47875 major capsid p AF ck: 2764 len: 1,503! Af Human papillomavirus type 6 clinical biopsy M46769 major capsid p AF ck: 2380 len: 1,503! Af Human papillomavirus type 6 clinical biopsy F50528 major capsid p AF ck: 2382 len: 1,503! Af Human papillomavirus type 6 clinical biopsy F50027 major capsid p
8 AF ck: 3578 len: 1,503! Af Human papillomavirus type 6 clinical biopsy F50602 major capsid p AF ck: 9856 len: 1,503! Af Human papillomavirus type 6 clinical biopsy M49898 major capsid p AF ck: 2262 len: 1,503! Af Human papillomavirus type 6 clinical biopsy M6 major capsid prote AF ck: 457 len: 1,503! Af Human papillomavirus type 6 clinical biopsy M44371 major capsid p AF ck: 955 len: 1,503! Af Human papillomavirus type 6 clinical biopsy M51033 major capsid p AF ck: 1413 len: 1,518! Af Human papillomavirus type 16 late major capsid protein (L1) gene, AF ck: 4448 len: 261! Af Human papillomavirus isolate HPVXS1 L1 protein gene, partial cds. 69: CACGG TGAGGAATATGATTTGCAATTTATATTTCAGTTGTGTA AAGTC AF ck: 2785 len: 8,012! Af Human papillomavirus type 6, complete genome. 10/1999 6,875: CATGT GGAAGAGTATGATTTACAATTTATTTTTCAATTATGTA GCATT AF ck: 8342 len: 7,904! Af Human papillomavirus type 16 isolate 16W12E, complete genome. 3/2 6,737: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA AF ck: 2413 len: 1,518! Af Human papillomavirus type 16 isolate Rochester capsid protein (L1
9 AF ck: 9994 len: 1,518! Af Human papillomavirus type 16 isolate GU1 capsid protein (L1) gene 1,101: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA ACATA AF ck: 1780 len: 1,518! Af Human papillomavirus type 16 isolate GU2 capsid protein (L1) gene AF ck: 2202 len: 1,518! Af Human papillomavirus type 16 capsid protein gene, complete cds. 6 D21208 ck: 1641 len: 7,801! D21208 Human papillomavirus type 67 complete genome. 2/1999 6,716: CATGT GGAAGAATATGATTTGCAGTTTATATTTCAGCTGTGCA AAATA HP ck: 5756 len: 449! U12492 Human papillomavirus type 67 L1 protein gene, My09/My11 region, par 153: CATGT GGAAGAATATGATTTGCAGTTTATATTTCAGCTGTGCA AAATA HP21941 ck: 6859 len: 7,905! U21941 Human papillomavirus type 70, complete genome. 3/2000 6,687: CATGT GGAGGAATATGATTTACAATTTATATTTCAATTGTGTA CTATC HP22461 ck: 2091 len: 3,283! U22461 Human papillomavirus type 70 E6 protein (E6), E7 protein (E7), and 1,129: CATGT GGAGGAATATGATTTACAATTTATATTTCAATTGTGTA CTATC HP34165 ck: 5614 len: 1,484! U34165 Human papillomavirus type 16, isolate NM 4094, late major capsid pr HP34166 ck: 5614 len: 1,484! U34166 Human papillomavirus type 16, isolate NM 9999, late major capsid pr HP34167 ck: 1493 len: 1,484! U34167 Human papillomavirus type 16, isolate NM T197, late major capsid pr
10 HP34168 ck: 1431 len: 1,484! U34168 Human papillomavirus type 16, isolate NM T446, late major capsid pr HP34169 ck: 2330 len: 1,484! U34169 Human papillomavirus type 16, isolate NM T455, late major capsid pr HP34170 ck: 5572 len: 1,484! U34170 Human papillomavirus type 16, isolate NM T529, late major capsid pr HP34171 ck: 666 len: 1,484! U34171 Human papillomavirus type 16, isolate OR 0198, late major capsid pr HP34172 ck: 3738 len: 1,484! U34172 Human papillomavirus type 16, isolate OR 1905, late major capsid pr HP34173 ck: 2238 len: 1,484! U34173 Human papillomavirus type 16, isolate OR 2087, late major capsid pr HP34174 ck: 4709 len: 1,484! U34174 Human papillomavirus type 16, isolate OR 3136, late major capsid pr HP34175 ck: 4390 len: 1,484! U34175 Human papillomavirus type 16, isolate OR 3473, late major capsid pr HP34176 ck: 4386 len: 1,484! U34176 Human papillomavirus type 16, isolate OR 3759, late major capsid pr
11 HP34177 ck: 5614 len: 1,484! U34177 Human papillomavirus type 16, isolate OR 4541, late major capsid pr HP34178 ck: 2238 len: 1,484! U34178 Human papillomavirus type 16, isolate OR 4716, late major capsid pr HP34179 ck: 2400 len: 1,484! U34179 Human papillomavirus type 16, isolate OR 4724, late major capsid pr HP34180 ck: 2400 len: 1,484! U34180 Human papillomavirus type 16, isolate OR 4997, late major capsid pr HP34181 ck: 2232 len: 1,484! U34181 Human papillomavirus type 16, isolate OR 5110, late major capsid pr HP34182 ck: 2238 len: 1,484! U34182 Human papillomavirus type 16, isolate OR 5428, late major capsid pr HP34183 ck: 5295 len: 1,484! U34183 Human papillomavirus type 16, isolate OR 6106, late major capsid pr HP34184 ck: 2232 len: 1,484! U34184 Human papillomavirus type 16, isolate OR 6170, late major capsid pr HP34185 ck: 2196 len: 1,484! U34185 Human papillomavirus type 16, isolate OR 6311, late major capsid pr HP34186 ck: 4390 len: 1,484! U34186 Human papillomavirus type 16, isolate OR 7145, late major capsid pr
12 HP34187 ck: 2242 len: 1,484! U34187 Human papillomavirus type 16, isolate OR 7574, late major capsid pr HP34188 ck: 4080 len: 1,484! U34188 Human papillomavirus type 16, isolate OR 7587, late major capsid pr HP34189 ck: 4437 len: 1,484! U34189 Human papillomavirus type 16, isolate OR 7632, late major capsid pr HP34190 ck: 5614 len: 1,484! U34190 Human papillomavirus type 16, isolate OR 8160, late major capsid pr HP34191 ck: 2400 len: 1,484! U34191 Human papillomavirus type 16, isolate OR 8329, late major capsid pr HP34192 ck: 2400 len: 1,484! U34192 Human papillomavirus type 16, isolate OR 8987, late major capsid pr HP34193 ck: 1523 len: 1,484! U34193 Human papillomavirus type 16, isolate OR 9237, late major capsid pr HP37217 ck: 7567 len: 2,920! U37217 Human papillomavirus type 16 variant L1 and L2 capsid protein genes 2,503: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA HP37488 ck: 8995 len: 7,759! U37488 Human papillomavirus type 54, complete genome. 11/1999 6,693: CATGT GGAGGAATATGATTTACAGTTTATATTTCAGTTATGTA CCATA HP45889 ck: 6619 len: 455! U45889 Human papillomavirus type 18, isolate IS002, major capsid protein L
13 159: CATGT TGAGGAATATGATTTGCAGTTTATTTTTCAGTTGTGTA CTATT HP45890 ck: 6811 len: 455! U45890 Human papillomavirus type 18, isolate IS326, major capsid protein L 159: CATGT TGAGGAATATGATTTGCAGTTTATTTTTCAGTTGTGTA CTATT HP45891 ck: 6369 len: 455! U45891 Human papillomavirus type 18, isolate IS664, major capsid protein L 159: CATGT TGAGGAATATGATTTGCAGTTTATTTTTCAGTTGTGTA CTATT HP45892 ck: 5761 len: 455! U45892 Human papillomavirus type 18, isolate IS168, major capsid protein L 159: CATGT TGAAGAATATGATTTGCAGTTTATTTTTCAGTTATGTA CTATT HP45893 ck: 5849 len: 455! U45893 Human papillomavirus type 18, isolate IS768, major capsid protein L 159: CATGT TGAAGAATATGATTTGCAGTTTATTTTTCAGTTATGTA CTATT HP45894 ck: 5941 len: 455! U45894 Human papillomavirus type 18, isolate IS172, major capsid protein L 159: CATGT TGAAGAATATGATTTGCAGTTTATTTTTCAGTTATGTA CTATT HP45897 ck: 3401 len: 449! U45897 Human papillomavirus type 33, isolate IS827, major capsid protein L 153: CATGT TGAAGAATATGATTTACAGTTTGTTTTTCAACTATGCA AAGTT HP45898 ck: 9542 len: 452! U45898 Human papillomavirus type 35, isolate IS071, major capsid protein L 156: CATGG TGAAGAATATGATTTACAGTTTATTTTTCAGTTATGTA AAATA HP45899 ck: 1099 len: 455! U45899 Human papillomavirus type 39, isolate IS270, major capsid protein L 159: CACGT GGAGGAGTATGATTTACAATTTATATTTCAACTGTGTA CTGTC HP45900 ck: 2703 len: 455! U45900 Human papillomavirus type 39, isolate IS073, major capsid protein L 159: CACGT GGAGGAGTATGATTTACAATTTATATTTCAACTGTGTA CTGTC HP45901 ck: 1677 len: 455! U45901 Human papillomavirus type 39, isolate IS114, major capsid protein L
14 159: CACGT GGAGGAGTATGATTTACAATTTATATTTCAACTGTGTA CTGTC HP45902 ck: 1929 len: 455! U45902 Human papillomavirus type 39, isolate IS065, major capsid protein L 159: CACGT GGAGGAGTATGATTTACAATTTATATTTCAACTGTGTA CTGTA HP45903 ck: 1972 len: 455! U45903 Human papillomavirus type 39, isolate IS015, major capsid protein L 159: CACGT GGAGGAGTATGATTTACAATTTATATTTCAACTGTGTA CTGTA HP45904 ck: 2212 len: 455! U45904 Human papillomavirus type 39, isolate IS214, major capsid protein L 159: CACGT GGAGGAGTATGATTTACAATTTATATTTCAACTGTGTA CTGTA HP45905 ck: 1515 len: 455! U45905 Human papillomavirus type 39, isolate IS351, major capsid protein L 159: CACGT GGAGGAGTATGATTTACAATTTATATTTCAACTGTGTA CTGTA HP45906 ck: 3282 len: 455! U45906 Human papillomavirus type 45, isolate IS816, major capsid protein L HP45907 ck: 3420 len: 455! U45907 Human papillomavirus type 45, isolate IS040, major capsid protein L HP45908 ck: 3324 len: 455! U45908 Human papillomavirus type 45, isolate IS282, major capsid protein L HP45909 ck: 3378 len: 455! U45909 Human papillomavirus type 45, isolate IS252, major capsid protein L HP45910 ck: 3318 len: 455! U45910 Human papillomavirus type 45, isolate IS819, major capsid protein L
15 HP45911 ck: 3489 len: 455! U45911 Human papillomavirus type 45, isolate IS949, major capsid protein L HP45912 ck: 3738 len: 455! U45912 Human papillomavirus type 45, isolate IS278, major capsid protein L HP45913 ck: 3618 len: 455! U45913 Human papillomavirus type 45, isolate IS894, major capsid protein L HP45914 ck: 3300 len: 455! U45914 Human papillomavirus type 45, isolate IS871, major capsid protein L HP45915 ck: 3468 len: 455! U45915 Human papillomavirus type 45, isolate IS788, major capsid protein L HP45916 ck: 3670 len: 455! U45916 Human papillomavirus type 45, isolate IS761, major capsid protein L HP45934 ck: 4322 len: 455! U45934 Human papillomavirus type 68, isolate IS362, major capsid protein L 159: CATGT TGAGGAATATGATTTGCAATTTATATTTCAGTTGTGTA CTATA HPA17206 ck: 4117 len: 455! Y17206 Human papillomavirus L1 gene, partial. 11/ : CATGT TGAGGAATATGATTTGCAATTCATATTTCAGTTGTGTA CTATA HPAF1600 ck: 1628 len: 4,550! Af Human papillomavirus type 16 integrated SiHa HPV-16 variant DNA, 3,421: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA HPAF3027 ck: 1911 len: 452! Af Human papillomavirus type 16 late major capsid protein L1 gene, p 156: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA
16 HPAF3028 ck: 1911 len: 452! Af Human papillomavirus type 16 late major capsid protein L1 gene, p 156: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA HPAF3029 ck: 1911 len: 452! Af Human papillomavirus type 16 late major capsid protein L1 gene, p 156: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA HPAF3030 ck: 1911 len: 452! Af Human papillomavirus type 16 late major capsid protein L1 gene, p 156: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA HPAF3031 ck: 1074 len: 1,486! Af Human papillomavirus type 16 late major capsid protein L1 gene, p 1,084: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA HPU89348 ck: 2434 len: 7,905! U89348 Human papillomavirus type 16 variant, complete sequence. 3/2000 6,738: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA HPU89349 ck: 8313 len: 5,210! U89349 Human papillomavirus type 18 variant, partial sequence. 12/ : CATGT TGAGGAATATGATTTGCAGTTTATTTTTCAGTTGTGTA CTATT HPV35H ck: 2592 len: 7,879! X74477 Human papillomavirus type 35H genomic DNA. 2/1999 6,695: CATGG TGAAGAATATGATTTACAGTTTATTTTTCAGTTATGTA AAATA HPV45 ck: 5657 len: 7,858! X74479 Human papillomavirus type 45 genomic DNA. 7/1997 6,720: CATGT GGAGGAATATGATTTACAGTTTATTTTTCAGTTGTGCA CTATT HPVL1 ck: 4360 len: 1,855! X67161 Human Papilloma Virus L1 gene for major capsid protein. 6/1996 1,297: CATGT TGAGGAATATGATTTGCAGTTTATATTTCAGTTGTGTA CTATA HSHPVME18 ck: 7395 len: 6,042! M73258 Human cellular DNA/Human papillomavirus proviral DNA. 6/2000
17 2,720: CATGT TGAGGAATATGATTTGCAATTTATATTTCAGTTGTGTA CTATA PA16 ck: 6074 len: 7,904! K02718 Human papillomavirus type 16 (HPV16), complete genome. 3/2000 6,737: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA PAHPV57 ck: 6613 len: 7,861! X55965 Human papillomavirus type 57 complete DNA. 4/1992 6,836: CATAT GGAGGAATATGATTTGCAGTTCATTTTTCAACTGTGCA AAATA PAPA6B ck: 3300 len: 7,902! X00203 Genital human papillomavirus type 6b (HPV6b). 7/1998 6,874: CATGT GGAAGAGTATGATTTACAATTTATTTTTCAATTATGTA GCATT PAPHPU111 ck: 3458 len: 455! U12486 Human papillomavirus isolate LVX160 L1 protein gene, My09/My11 regi 159: CATGT GGAGGAATATGATTTACAATTTATATTTCAATTGTGTA CTATC PAPHPU124 ck: 4196 len: 455! U12476 Human papillomavirus isolate CP141 L1 protein gene, My09/My11 regio 159: CATGT GGAGGAATATGATTTACAATTTATATTTCAATTGTGTA CTATC PAPHPV18 ck: 4890 len: 7,857! X05015 Human papillomavirus type 18 E6, E7, E1, E2, E4, E5, L1 & L2 genes. 6,716: CATGT TGAGGAATATGATTTGCAGTTTATTTTTCAGTTGTGTA CTATT PAPPPH35C ck: 9551 len: 7,851! M74117 Human papillomavirus type 35 complete genome. 3/2000 6,677: CATGG TGAAGAATATGATTTACAGTTTATTTTTCAGTTATGTA AAATA PAPPPHE61 ck: 6716 len: 8,010! L41216 Human papillomavirus, type 6a, complete genome. 3/2000 6,875: CATGT GGAAGAGTATGATTTACAATTTATTTTTCAATTATGTA GCATT PAPPPVT3 ck: 5647 len: 7,833! M62849 Human papillomavirus ORFs. 3/2000 6,743: CACGT GGAGGAGTATGATTTACAATTTATATTTCAACTGTGTA CTGTC PAPU01535 ck: 2985 len: 415! U01535 Human papillomavirus PCR type AE1 sequence. 3/2000
18 139: CATGT GGAGGAATATGATTTACAATTTATATTTCAATTGTGTA CTATC S65833 ck: 9472 len: 356! S65833 {L1 region, squamous vulvar cancer isolate} [human papillomavirus t 108: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA S65837 ck: 4819 len: 329! S65837 {L1 region, verrucous cancer of foot isolate} [human papillomavirus 95: CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA S71514 ck: 1729 len: 452! S71514 L1 [human papillomavirus type 16 HPV16, Genomic, 452 nt]. 3/ : CATGG GGAGGAATATGATTTACAGTTTATTTTTCAACTGTGCA AAATA S73503 ck: 2502 len: 449! S73503 L1 [human papillomaviruse type 6 HPV Manuela, Genomic, 449 nt]. 3/ : CATGT GGAAGAGTATGATTTACAATTTATTTTTCAATTATGTA GCATT Ansprüche 1.) Diesen Nukleinsäurepool in molekularbiologischen Verfahren, wie zum Beispiel der Hybridisierung, zu verwenden.
Molekulargenetischer Nachweis und Genotypisierung von HPV
 Molekulargenetischer Nachweis und Genotypisierung von HPV Dr. Sabine Sussitz-Rack Institut für Labordiagnostik und Mikrobiologie Vorstand: Prim. Prof. DDr. Pranav Sinha Humanes Papillomavirus HPV HPV ist
Molekulargenetischer Nachweis und Genotypisierung von HPV Dr. Sabine Sussitz-Rack Institut für Labordiagnostik und Mikrobiologie Vorstand: Prim. Prof. DDr. Pranav Sinha Humanes Papillomavirus HPV HPV ist
Neue DNA Sequenzierungstechnologien im Überblick
 Neue DNA Sequenzierungstechnologien im Überblick Dr. Bernd Timmermann Next Generation Sequencing Core Facility Max Planck Institute for Molecular Genetics Berlin, Germany Max-Planck-Gesellschaft 80 Institute
Neue DNA Sequenzierungstechnologien im Überblick Dr. Bernd Timmermann Next Generation Sequencing Core Facility Max Planck Institute for Molecular Genetics Berlin, Germany Max-Planck-Gesellschaft 80 Institute
Molekularbiologische Datenbanken
 Molekularbiologische Datenbanken Übungen Sommersemester 2004 Silke Trißl Prof. Ulf Leser Wissensmanagement in der Bioinformatik Organisatorisches Mittwoch 11 13 Uhr, RUD26 0'313 Mi, 05. Mai 2004 entfällt
Molekularbiologische Datenbanken Übungen Sommersemester 2004 Silke Trißl Prof. Ulf Leser Wissensmanagement in der Bioinformatik Organisatorisches Mittwoch 11 13 Uhr, RUD26 0'313 Mi, 05. Mai 2004 entfällt
HPV DNA-Chip. PapilloCheck HPV-Screening. DNA-Chip für die Identifizierung von 24 humanen Papillomavirus Typen
 HPV DNA-Chip PapilloCheck HPV-Screening DNA-Chip für die Identifizierung von 24 humanen Papillomavirus Typen PapilloCheck : schnell und zuverlässig PapilloCheck im Überblick Komplettes Kit mit DNA-Arrays
HPV DNA-Chip PapilloCheck HPV-Screening DNA-Chip für die Identifizierung von 24 humanen Papillomavirus Typen PapilloCheck : schnell und zuverlässig PapilloCheck im Überblick Komplettes Kit mit DNA-Arrays
MOL.504 Analyse von DNA- und Proteinsequenzen. Übungsaufgaben Datenbanken und Informationssysteme
 MOL.504 Analyse von DNA- und Proteinsequenzen Übungsaufgaben Datenbanken und Informationssysteme Ü1 Tutorial für NCBI NCBI Nucleotide: Suche nach cellobiose dehydrogenase fungi Ü1 Tutorial für NCBI NCBI
MOL.504 Analyse von DNA- und Proteinsequenzen Übungsaufgaben Datenbanken und Informationssysteme Ü1 Tutorial für NCBI NCBI Nucleotide: Suche nach cellobiose dehydrogenase fungi Ü1 Tutorial für NCBI NCBI
Gebärmutterhalskrebs. Was Sie zur Vorsorge tun können!
 Gebärmutterhalskrebs verhüten Was Sie zur Vorsorge tun können! GEBÄRMUTTERHALSKREBS Die Zervix ist der Gebärmutterhals, also der untere Teil der Gebärmutter, der die Öffnung zur Scheide, den Muttermund,
Gebärmutterhalskrebs verhüten Was Sie zur Vorsorge tun können! GEBÄRMUTTERHALSKREBS Die Zervix ist der Gebärmutterhals, also der untere Teil der Gebärmutter, der die Öffnung zur Scheide, den Muttermund,
Einblicke in das menschliche Erbgut (Genom) am Computer
 Einblicke in das menschliche Erbgut (Genom) am Computer Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de Binger Nacht der Wissenschaft - 16.04.2010 Das menschliche Genom ist entschlüsselt
Einblicke in das menschliche Erbgut (Genom) am Computer Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de Binger Nacht der Wissenschaft - 16.04.2010 Das menschliche Genom ist entschlüsselt
HPV- Feigwarzen- Analkrebs
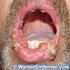 HPV- Feigwarzen- Analkrebs Kurzer Überblick Luca Daniel Stein Gemeinschafts-Praxis: Jessen- Jessen- Stein, Motzstr. 19, 10777 Berlin HPV Was ist das? Humanes Papilloma Virus 1983 findet zur Hausen in Heidelberg
HPV- Feigwarzen- Analkrebs Kurzer Überblick Luca Daniel Stein Gemeinschafts-Praxis: Jessen- Jessen- Stein, Motzstr. 19, 10777 Berlin HPV Was ist das? Humanes Papilloma Virus 1983 findet zur Hausen in Heidelberg
Zielgerichtete Therapie mit Olaparib bei BRCA1/2- Mutationsträgerinnen
 Zielgerichtete Therapie mit Olaparib bei BRCA1/2- Mutationsträgerinnen Prof. Dr. med. Brigitte Schlegelberger 670513011/15 Olaparib Zulassung in Europa: Rezidiv eines Platin-sensitiven Ovarialkarzinoms
Zielgerichtete Therapie mit Olaparib bei BRCA1/2- Mutationsträgerinnen Prof. Dr. med. Brigitte Schlegelberger 670513011/15 Olaparib Zulassung in Europa: Rezidiv eines Platin-sensitiven Ovarialkarzinoms
Evolution & Genetik (Beispiel Hämoglobin) Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de
 Evolution & Genetik (Beispiel Hämoglobin) Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de DNA (Desoxyribonukleinsäure) 5 3 CGATGTACATCG GCTACATGTAGC 3 5 Doppelhelix Basen: Adenin,
Evolution & Genetik (Beispiel Hämoglobin) Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de DNA (Desoxyribonukleinsäure) 5 3 CGATGTACATCG GCTACATGTAGC 3 5 Doppelhelix Basen: Adenin,
Was ist Bioinformatik?
 9. Kurstag: Bioinformatik Der Begriff "Bioinformatik" wurde 1989 erstmals von D.R. Masys im JOURNAL OF RESEARCH OF THE NATIONAL INSTITUTE OF STANDARDS AND TECHNOLOGY erwähnt. Was ist Bioinformatik? Die
9. Kurstag: Bioinformatik Der Begriff "Bioinformatik" wurde 1989 erstmals von D.R. Masys im JOURNAL OF RESEARCH OF THE NATIONAL INSTITUTE OF STANDARDS AND TECHNOLOGY erwähnt. Was ist Bioinformatik? Die
Papillomaviridae. Typ. 16 Genera 118 Typen. Spezies. Papillomaviridae. Molekulare Virologie
 Typ 16 Genera 118 Typen Spezies 45-60 % 60-70 % 75-90 % > 90 % De Villiers et al.,2004, Virology 324,17-27. Papillomavirus Besonderes Merkmal: Sehr ausgeprägte Wirts- und Gewebe-Spezifität: Replikation
Typ 16 Genera 118 Typen Spezies 45-60 % 60-70 % 75-90 % > 90 % De Villiers et al.,2004, Virology 324,17-27. Papillomavirus Besonderes Merkmal: Sehr ausgeprägte Wirts- und Gewebe-Spezifität: Replikation
Mutations. Ploidy mutations. Hypoploidy (e.g. Monosomy) Hyperploidy (e.g. Trisomy. Effects: mostly pleiotropic or loss of function
 Mutations Intragenic (gene) mutations Base substitutions Transversions Pu Py Transitions Pu Pu or Py Py Insertions (small) Deletions (small) Effects: Change or loss of function of single genes, Mutation
Mutations Intragenic (gene) mutations Base substitutions Transversions Pu Py Transitions Pu Pu or Py Py Insertions (small) Deletions (small) Effects: Change or loss of function of single genes, Mutation
Zusätzliche Behandlungs möglichkeiten für Ihre Patienten
 Zusätzliche Behandlungs möglichkeiten für Ihre Patienten Über FoundationOne Bei dem validierten umfassenden Tumorprofil von FoundationOne wird die gesamte codierende Sequenz von 315 krebsassoziierten Genen
Zusätzliche Behandlungs möglichkeiten für Ihre Patienten Über FoundationOne Bei dem validierten umfassenden Tumorprofil von FoundationOne wird die gesamte codierende Sequenz von 315 krebsassoziierten Genen
HPV-Impfung, führt sie zu einer Revolution der gynäkologischen Vorsorge?
 HPV-Impfung, führt sie zu einer Revolution der gynäkologischen Vorsorge? HPV-Impfung, führt sie zu einer Revolution der gynäkologischen Vorsorge? Gynäkologische Vorsorge der Erreger Übertragung Problem
HPV-Impfung, führt sie zu einer Revolution der gynäkologischen Vorsorge? HPV-Impfung, führt sie zu einer Revolution der gynäkologischen Vorsorge? Gynäkologische Vorsorge der Erreger Übertragung Problem
AGES-Webribo. Systematik in Clostridium difficile PCR-Ribotyping. Alexander Indra
 AGES-Webribo Systematik in Clostridium difficile PCR-Ribotyping Alexander Indra AGES-Institut für medizinische Mikrobiologie und Hygiene Wien Nationale Referenzzentrale für Clostridium difficile Clostridium
AGES-Webribo Systematik in Clostridium difficile PCR-Ribotyping Alexander Indra AGES-Institut für medizinische Mikrobiologie und Hygiene Wien Nationale Referenzzentrale für Clostridium difficile Clostridium
RNA und Expression RNA
 RNA und Expression Biochemie RNA 1) Die Transkription. 2) RNA-Typen 3) RNA Funktionen 4) RNA Prozessierung 5) RNA und Proteinexpression/Regelung 1 RNA-Typen in E. coli Vergleich RNA-DNA Sequenz 2 Die Transkriptions-Blase
RNA und Expression Biochemie RNA 1) Die Transkription. 2) RNA-Typen 3) RNA Funktionen 4) RNA Prozessierung 5) RNA und Proteinexpression/Regelung 1 RNA-Typen in E. coli Vergleich RNA-DNA Sequenz 2 Die Transkriptions-Blase
Kursinhalte der Weiterbildung Molekulare Biotechnologie (MNr.: 237 / 0411 / 2010)
 Kursinhalte der Weiterbildung Molekulare Biotechnologie (MNr.: 237 / 0411 / 2010) Schwerpunkte im Bereich BIOANALYTIK Polyacrylamidelektrophorese von Nukleinsäuren im Vertikalsystem Agarosegelelektrophorese
Kursinhalte der Weiterbildung Molekulare Biotechnologie (MNr.: 237 / 0411 / 2010) Schwerpunkte im Bereich BIOANALYTIK Polyacrylamidelektrophorese von Nukleinsäuren im Vertikalsystem Agarosegelelektrophorese
Personalisierte Medizin
 Personalisierte Medizin Möglichkeiten und Grenzen Prof. Dr. Friedemann Horn Universität Leipzig, Institut für Klinische Immunologie, Molekulare Immunologie Fraunhofer Institut für Zelltherapie und Immunologie
Personalisierte Medizin Möglichkeiten und Grenzen Prof. Dr. Friedemann Horn Universität Leipzig, Institut für Klinische Immunologie, Molekulare Immunologie Fraunhofer Institut für Zelltherapie und Immunologie
Sequenziertechnologien
 Sequenziertechnologien Folien teilweise von G. Thallinger übernommen 11 Entwicklung der Sequenziertechnologie First Generation 1977 Sanger Sequenzierung (GOLD Standard) Second Generation 2005 454 Sequencing
Sequenziertechnologien Folien teilweise von G. Thallinger übernommen 11 Entwicklung der Sequenziertechnologie First Generation 1977 Sanger Sequenzierung (GOLD Standard) Second Generation 2005 454 Sequencing
Übung II. Einführung, Teil 1. Arbeiten mit Ensembl
 Übung II Einführung, Teil 1 Arbeiten mit Ensembl Ensembl Genome Browser (Bereitstellung von Vielzeller Genomen) Projekt wurde 1999 initiiert Projektpartner EMBL European Bioinformatics Institute (EBI)
Übung II Einführung, Teil 1 Arbeiten mit Ensembl Ensembl Genome Browser (Bereitstellung von Vielzeller Genomen) Projekt wurde 1999 initiiert Projektpartner EMBL European Bioinformatics Institute (EBI)
Evidence of strobilurine resistant isolates of A. solani and A. alternata in Germany
 Technische Universität München Evidence of strobilurine resistant isolates of A. solani and A. alternata in Germany H. Hausladen, B. Adolf and J. Leiminger outline introduction material and methods results
Technische Universität München Evidence of strobilurine resistant isolates of A. solani and A. alternata in Germany H. Hausladen, B. Adolf and J. Leiminger outline introduction material and methods results
Bivalvia - Bivalves - Muscheln. Band 3
 Bivalvia - Bivalves - Muscheln Band 3 Uwe Kraeft & Michael Kraeft 2016 Berichte aus der Geowissenschaft Uwe Kraeft & Michael Kraeft Bivalvia - Bivalves - Muscheln Band 3 Shaker Verlag Aachen 2016 Bibliografische
Bivalvia - Bivalves - Muscheln Band 3 Uwe Kraeft & Michael Kraeft 2016 Berichte aus der Geowissenschaft Uwe Kraeft & Michael Kraeft Bivalvia - Bivalves - Muscheln Band 3 Shaker Verlag Aachen 2016 Bibliografische
Jahreshauptversammlung 2010. Bericht aus Kiel
 Jahreshauptversammlung 2010 Bericht aus Kiel Wolfram Klapper & Reiner Siebert Bericht aus Kiel 2010... Die KKI-Labore in Kiel: Ziele der Forschungsprojekte Der LightCycler: ein neues Großgerät in 2009
Jahreshauptversammlung 2010 Bericht aus Kiel Wolfram Klapper & Reiner Siebert Bericht aus Kiel 2010... Die KKI-Labore in Kiel: Ziele der Forschungsprojekte Der LightCycler: ein neues Großgerät in 2009
Biotechnologische Arzneimittel Von der Herstellung zur Anwendung
 Biotechnologische Arzneimittel Von der Herstellung zur Anwendung Abbildungen, Diagramme, Tabellen Acetylsalicylsäure Insulin monoklonaler Antikörper (ASS) 21 Atome 788 Atome ca. 20.000 Atome Größenvergleich
Biotechnologische Arzneimittel Von der Herstellung zur Anwendung Abbildungen, Diagramme, Tabellen Acetylsalicylsäure Insulin monoklonaler Antikörper (ASS) 21 Atome 788 Atome ca. 20.000 Atome Größenvergleich
Informationsmaterial Resistenz gegen HIV Recherche und Analyse molekularer Daten
 1 Informationsmaterial Resistenz gegen HIV Recherche und Analyse molekularer Daten (inkl. Anleitungen zur Recherche von Sequenzen mit GenBank und zur Analyse mit GeneDoc) In der Computer-basierten Version
1 Informationsmaterial Resistenz gegen HIV Recherche und Analyse molekularer Daten (inkl. Anleitungen zur Recherche von Sequenzen mit GenBank und zur Analyse mit GeneDoc) In der Computer-basierten Version
VORKOMMEN VON ANTIBIOTIKA- RESISTENZGENEN UND EFFIZIENZ UNTERSCHIEDLICHER BEHANDLUNGSVERFAHREN (O 3, CL 3, UV)
 VORKOMMEN VON ANTIBIOTIKA- RESISTENZGENEN UND EFFIZIENZ UNTERSCHIEDLICHER BEHANDLUNGSVERFAHREN (O 3, CL 3, UV) Dipl.-Ing. (FH) Claudia Stange, Prof. Dr. Andreas Tiehm Nachweismethoden von Antibiotikaresistenzen
VORKOMMEN VON ANTIBIOTIKA- RESISTENZGENEN UND EFFIZIENZ UNTERSCHIEDLICHER BEHANDLUNGSVERFAHREN (O 3, CL 3, UV) Dipl.-Ing. (FH) Claudia Stange, Prof. Dr. Andreas Tiehm Nachweismethoden von Antibiotikaresistenzen
Vorlesung Molekulare Humangenetik
 Vorlesung Molekulare Humangenetik WS 2013/2014 Dr. Shamsadin DNA-RNA-Protein Allgemeines Prüfungen o. Klausuren als indiv. Ergänzung 3LP benotet o. unbenotet Seminar Block 2LP Vorlesung Donnerstags 14-16
Vorlesung Molekulare Humangenetik WS 2013/2014 Dr. Shamsadin DNA-RNA-Protein Allgemeines Prüfungen o. Klausuren als indiv. Ergänzung 3LP benotet o. unbenotet Seminar Block 2LP Vorlesung Donnerstags 14-16
Unsere Testparameter für Ihr PCR-Labor
 Unsere Testparameter für Ihr PCR-Labor Tests für die in-vitro-diagnostik CE-IVD validierte Analyse von der Probenaufarbeitung bis zur Ergebnisausgabe Parameter Testtypus Analysesystem Probenmaterial Testspezifikationen
Unsere Testparameter für Ihr PCR-Labor Tests für die in-vitro-diagnostik CE-IVD validierte Analyse von der Probenaufarbeitung bis zur Ergebnisausgabe Parameter Testtypus Analysesystem Probenmaterial Testspezifikationen
Molekularbiologische Methoden
 Molekularbiologische Methoden im Lebensmittel-Labor Dr. rer. nat. Armin Pahl LADR GmbH MVZ Dr. Kramer & Kollegen 04152 803-0 www.ladr.de DNA 1866 Gregor Mendel veröffentlicht seine Versuche über Pflanzen-Hybriden,
Molekularbiologische Methoden im Lebensmittel-Labor Dr. rer. nat. Armin Pahl LADR GmbH MVZ Dr. Kramer & Kollegen 04152 803-0 www.ladr.de DNA 1866 Gregor Mendel veröffentlicht seine Versuche über Pflanzen-Hybriden,
MOL.504 Analyse von DNA- und Proteinsequenzen
 MOL.504 Analyse von DNA- und Proteinsequenzen Kurs 1 Monika Oberer, Karl Gruber MOL.504 Modul-Übersicht Einführung, Datenbanken BLAST-Suche, Sequenzalignment Proteinstrukturen Virtuelles Klonieren Abschlusstest
MOL.504 Analyse von DNA- und Proteinsequenzen Kurs 1 Monika Oberer, Karl Gruber MOL.504 Modul-Übersicht Einführung, Datenbanken BLAST-Suche, Sequenzalignment Proteinstrukturen Virtuelles Klonieren Abschlusstest
Inhalt. Entdeckung und allgemeine Informationen. Klassifizierung. Genom Viren untypische Gene Tyrosyl-tRNA Synthetase. Ursprung von grossen DNA Viren
 Mimivirus Inhalt Entdeckung und allgemeine Informationen Klassifizierung Genom Viren untypische Gene Tyrosyl-tRNA Synthetase Ursprung von grossen DNA Viren Entstehung von Eukaryoten Entdeckung 1992 in
Mimivirus Inhalt Entdeckung und allgemeine Informationen Klassifizierung Genom Viren untypische Gene Tyrosyl-tRNA Synthetase Ursprung von grossen DNA Viren Entstehung von Eukaryoten Entdeckung 1992 in
Resistenz gegen HIV (Computer- und Internet-basierte Aufgabe)
 1 Resistenz gegen HIV (Computer- und Internet-basierte Aufgabe) In den frühen 1990er Jahren zeigten verschiedene Untersuchungen, dass einige Menschen trotz wiederholten Kontaktes mit dem HI-Virus nicht
1 Resistenz gegen HIV (Computer- und Internet-basierte Aufgabe) In den frühen 1990er Jahren zeigten verschiedene Untersuchungen, dass einige Menschen trotz wiederholten Kontaktes mit dem HI-Virus nicht
Ergebnisse 32. Peptid 1- Peptid 2- Peptid 1- Peptid 2- Sepharose Sepharose Sepharose Sepharose 1/I 1/II 2/I 2/II
 Ergebnisse 32 4 Ergebnisse 4.1 Nachweis des ORF1-Proteins p40 Das erste offene Leseraster (ORF1) eines L1-Retrotransposons kodiert für ein 40 kd Protein (p40-protein). Dieses Protein hat eine Chaperone-Funktion
Ergebnisse 32 4 Ergebnisse 4.1 Nachweis des ORF1-Proteins p40 Das erste offene Leseraster (ORF1) eines L1-Retrotransposons kodiert für ein 40 kd Protein (p40-protein). Dieses Protein hat eine Chaperone-Funktion
Horizontaler Gentransfer. Referentin: Michaela Baune Seminar: Gentechnik in der Landwirtschaft
 Horizontaler Gentransfer Referentin: Michaela Baune Seminar: Gentechnik in der Landwirtschaft 28.06.2016 2 Einleitung Abb. 1 3 Einleitung Befürchtung: Übertragung von Antibiotikaresistenzen von transgenen
Horizontaler Gentransfer Referentin: Michaela Baune Seminar: Gentechnik in der Landwirtschaft 28.06.2016 2 Einleitung Abb. 1 3 Einleitung Befürchtung: Übertragung von Antibiotikaresistenzen von transgenen
27 Funktionelle Genomanalysen Sachverzeichnis
 Inhaltsverzeichnis 27 Funktionelle Genomanalysen... 543 27.1 Einleitung... 543 27.2 RNA-Interferenz: sirna/shrna-screens 543 Gunter Meister 27.3 Knock-out-Technologie: homologe Rekombination im Genom der
Inhaltsverzeichnis 27 Funktionelle Genomanalysen... 543 27.1 Einleitung... 543 27.2 RNA-Interferenz: sirna/shrna-screens 543 Gunter Meister 27.3 Knock-out-Technologie: homologe Rekombination im Genom der
Liquid Biopsy-Diagnostik von zellfreier DNA und zirkulierenden Tumorzellen: "Hip or Hype"
 Liquid Biopsy-Diagnostik von zellfreier DNA und zirkulierenden Tumorzellen: "Hip or Hype" 3. Nationales Biobankensymposium 2014 Berlin, 04.12.2014 Prof. Dr. rer. nat Edgar Dahl RWTH zentralisierte Biomaterialbank
Liquid Biopsy-Diagnostik von zellfreier DNA und zirkulierenden Tumorzellen: "Hip or Hype" 3. Nationales Biobankensymposium 2014 Berlin, 04.12.2014 Prof. Dr. rer. nat Edgar Dahl RWTH zentralisierte Biomaterialbank
Softwarewerkzeuge der. Bioinformatik
 Bioinformatik Wintersemester 2006/2007 Tutorial 1: Biologische Datenbanken SRS Tutorial 1: Datenbanken 1/22 Sequenzquellen DNA- Sequenzierung Protein- Sequenzierung Translation Proteinsequenzen Tutorial
Bioinformatik Wintersemester 2006/2007 Tutorial 1: Biologische Datenbanken SRS Tutorial 1: Datenbanken 1/22 Sequenzquellen DNA- Sequenzierung Protein- Sequenzierung Translation Proteinsequenzen Tutorial
Die Paten)erbarkeit von Gensequenzen - von Biomarkern. Prof. Dr. iur. Dr. rer. pol. Jürgen Ensthaler, TU Berlin
 Die Paten)erbarkeit von Gensequenzen - von Biomarkern Prof. Dr. iur. Dr. rer. pol. Jürgen Ensthaler, TU Berlin Was sind Biomarker? Defini)on: Ø Es gibt noch keine einheitliche Defini)on für Biomarker.
Die Paten)erbarkeit von Gensequenzen - von Biomarkern Prof. Dr. iur. Dr. rer. pol. Jürgen Ensthaler, TU Berlin Was sind Biomarker? Defini)on: Ø Es gibt noch keine einheitliche Defini)on für Biomarker.
DNA Replikation ist semikonservativ. Abb. aus Stryer (5th Ed.)
 DNA Replikation ist semikonservativ Entwindung der DNA-Doppelhelix durch eine Helikase Replikationsgabel Eltern-DNA Beide DNA-Stränge werden in 5 3 Richtung synthetisiert DNA-Polymerasen katalysieren die
DNA Replikation ist semikonservativ Entwindung der DNA-Doppelhelix durch eine Helikase Replikationsgabel Eltern-DNA Beide DNA-Stränge werden in 5 3 Richtung synthetisiert DNA-Polymerasen katalysieren die
Auffälliger Vorsorgeabstrich Humane Papillomaviren
 Auffälliger Vorsorgeabstrich Humane Papillomaviren Sehr geehrte Patientinnen, die meisten Erwachsenen kommen während ihres Lebens mit humanen Papillomaviren (HPV) in Kontakt. 70 Prozent aller Frauen stecken
Auffälliger Vorsorgeabstrich Humane Papillomaviren Sehr geehrte Patientinnen, die meisten Erwachsenen kommen während ihres Lebens mit humanen Papillomaviren (HPV) in Kontakt. 70 Prozent aller Frauen stecken
FOR MUW SSM3 (2008) STUDENTS EDUCATIONAL PURPOSE ONLY
 Angewandte Bioinformatik Grundlagen der Annotation von eukaryotischen Genomen Online Datenbanken und Bioinformatik Tools Sequenzen Sequenzalignment: Fasta und Blast Motive und Hidden Markov Models Genom-Browser
Angewandte Bioinformatik Grundlagen der Annotation von eukaryotischen Genomen Online Datenbanken und Bioinformatik Tools Sequenzen Sequenzalignment: Fasta und Blast Motive und Hidden Markov Models Genom-Browser
Die perfekte Kombination. Effektive Biomarker-Kombination zur Früherkennung von hochgradigen Vorstufen des Zervixkarzinoms
 Früherkennung des Zervixkarzinoms: Die perfekte Kombination. Effektive Biomarker-Kombination zur Früherkennung von hochgradigen Vorstufen des Zervixkarzinoms p16 PLUS Ki-67 in einem einzelnen Test CLARITY
Früherkennung des Zervixkarzinoms: Die perfekte Kombination. Effektive Biomarker-Kombination zur Früherkennung von hochgradigen Vorstufen des Zervixkarzinoms p16 PLUS Ki-67 in einem einzelnen Test CLARITY
UKD Universitätsklinikum
 Vortragsreihe mit praxisnahen Beispielen und Über- sichten zu NGS- Lösungsansätzen sowie anschlies- sender Diskussion und praxisorienberten Demos. Datum Uhrzeit Vortrag / Unternehmen Referent DI 09. Juni
Vortragsreihe mit praxisnahen Beispielen und Über- sichten zu NGS- Lösungsansätzen sowie anschlies- sender Diskussion und praxisorienberten Demos. Datum Uhrzeit Vortrag / Unternehmen Referent DI 09. Juni
Der HPV-Test verschafft Sicherheit. So schützen Sie sich vor Gebärmutterhalskrebs
 Der HPV-Test verschafft Sicherheit So schützen Sie sich vor Gebärmutterhalskrebs Section title Was ist HPV? Bereits 1986 identifizierte der deutsche Krebsforscher Professor Harald zur Hausen humane Papillomviren
Der HPV-Test verschafft Sicherheit So schützen Sie sich vor Gebärmutterhalskrebs Section title Was ist HPV? Bereits 1986 identifizierte der deutsche Krebsforscher Professor Harald zur Hausen humane Papillomviren
Organisation und Evolution des Genoms
 Organisation und Evolution des Genoms Organisation und Evolution des Genoms Definition Genom: vollständige DNA-Sequenz eines Organismus I. Einfachstes Genom: Prokaryoten Zwei Gruppen, evolutionär unterschiedlicher
Organisation und Evolution des Genoms Organisation und Evolution des Genoms Definition Genom: vollständige DNA-Sequenz eines Organismus I. Einfachstes Genom: Prokaryoten Zwei Gruppen, evolutionär unterschiedlicher
Sie haben die Möglichkeit, an dieser Impfaktion teilzunehmen, wenn Sie folgende Voraussetzungen erfüllen:
 HPV- Impfkampagne Liebe Niederösterreicherin! Das Land Niederösterreich fördert als erstes Bundesland auf Initiative von Landeshauptmann Dr. Erwin Pröll Impfungen gegen HPV (=humane Papillomviren), die
HPV- Impfkampagne Liebe Niederösterreicherin! Das Land Niederösterreich fördert als erstes Bundesland auf Initiative von Landeshauptmann Dr. Erwin Pröll Impfungen gegen HPV (=humane Papillomviren), die
PD Dr. med. Christian Meisel Site Leader Oncology & Head Translational Medicine Roche Pharma Research and Early Development, Penzberg
 Personalisierte Medizin - Status und Zukunft PD Dr. med. Christian Meisel Site Leader Oncology & Head Translational Medicine Roche Pharma Research and Early Development, Penzberg Personalisierte Medizin
Personalisierte Medizin - Status und Zukunft PD Dr. med. Christian Meisel Site Leader Oncology & Head Translational Medicine Roche Pharma Research and Early Development, Penzberg Personalisierte Medizin
VORANGEGANGENE MODELLE
 VORANGEGANGENE MODELLE UNSER THEMA HEUTE Ziel dieses Papers: - Nähere Charakterisierung der AuxREs - Analyse eines zu den AuxREs gehörenden Transkriptionsfaktors WAS BEREITS BEKANNT WAR: - Auxin moduliert
VORANGEGANGENE MODELLE UNSER THEMA HEUTE Ziel dieses Papers: - Nähere Charakterisierung der AuxREs - Analyse eines zu den AuxREs gehörenden Transkriptionsfaktors WAS BEREITS BEKANNT WAR: - Auxin moduliert
Anlage zur Akkreditierungsurkunde D PL 13372 01 00
 Deutsche Akkreditierungsstelle GmbH Anlage zur Akkreditierungsurkunde D PL 13372 01 00 nach DIN EN ISO/IEC 17025:2005 Gültigkeitsdauer: 22.05.2014 bis 25.03.2017 Ausstellungsdatum: 22.05.2014 Urkundeninhaber:
Deutsche Akkreditierungsstelle GmbH Anlage zur Akkreditierungsurkunde D PL 13372 01 00 nach DIN EN ISO/IEC 17025:2005 Gültigkeitsdauer: 22.05.2014 bis 25.03.2017 Ausstellungsdatum: 22.05.2014 Urkundeninhaber:
Wenn Viren Krebs verursachen. Das Humane Papilloma Virus und die Entstehung von Mund und Rachenkrebs
 Wenn Viren Krebs verursachen Das Humane Papilloma Virus und die Entstehung von Mund und Rachenkrebs Prevo Check der Schnelltest zur Früherkennung von HPV16+ Mund und Rachenkrebs Dr. Ralf Hilfrich BWKrkhs
Wenn Viren Krebs verursachen Das Humane Papilloma Virus und die Entstehung von Mund und Rachenkrebs Prevo Check der Schnelltest zur Früherkennung von HPV16+ Mund und Rachenkrebs Dr. Ralf Hilfrich BWKrkhs
Mitteilung an die Medien
 Mitteilung an die Medien Branford, CT, USA, 29. Januar 2009 Forscher nutzen das 454 Sequencing System bei der Identifizierung Herpesähnlicher Viren in Zusammenhang mit Korallensterben Mit metagenomischen
Mitteilung an die Medien Branford, CT, USA, 29. Januar 2009 Forscher nutzen das 454 Sequencing System bei der Identifizierung Herpesähnlicher Viren in Zusammenhang mit Korallensterben Mit metagenomischen
Modell eines HPV-Capsids
 Ausschneidebogen: Modell eines HPV-Capsids Hinweis: kartonstarkes Papier mit mindestens 170 g/m² ist am besten geeignet Schneiden Sie die Vorlage aus 20 gleichseitigen Dreiecken (grau) mit den Falzen (weiß)
Ausschneidebogen: Modell eines HPV-Capsids Hinweis: kartonstarkes Papier mit mindestens 170 g/m² ist am besten geeignet Schneiden Sie die Vorlage aus 20 gleichseitigen Dreiecken (grau) mit den Falzen (weiß)
Winterschool Obergurgl. Molekulare Typisierung CF-relevanter Erreger
 Winterschool Obergurgl Molekulare Typisierung CF-relevanter Erreger Barbara C. Kahl Institut für Medizinische Mikrobiologie Universitätsklinikum Münster Warum Typisierung? Individueller Patient Persistierende
Winterschool Obergurgl Molekulare Typisierung CF-relevanter Erreger Barbara C. Kahl Institut für Medizinische Mikrobiologie Universitätsklinikum Münster Warum Typisierung? Individueller Patient Persistierende
Expressionskontrolle in Eukaryonten
 Expressionskontrolle in Eukaryonten Warum muss Genexpression kontrolliert werden? 1. Gewebsspezifische Kontrolle - nicht jedes Genprodukt ist in allen Zellen erforderlich - manche Genprodukte werden ausschliesslich
Expressionskontrolle in Eukaryonten Warum muss Genexpression kontrolliert werden? 1. Gewebsspezifische Kontrolle - nicht jedes Genprodukt ist in allen Zellen erforderlich - manche Genprodukte werden ausschliesslich
Genforschung, Gentechnologie, Gentherapie. Referat: Sarah Hohenbrink Philipp Kappel Fleur Lebhardt VS Hans-Jürgen Osigus
 Genforschung, Gentechnologie, Gentherapie Referat: Sarah Hohenbrink Philipp Kappel Fleur Lebhardt VS Hans-Jürgen Osigus Genforschung Gentechnik Gentherapie Human Genome Project Patentierung Gentechnik
Genforschung, Gentechnologie, Gentherapie Referat: Sarah Hohenbrink Philipp Kappel Fleur Lebhardt VS Hans-Jürgen Osigus Genforschung Gentechnik Gentherapie Human Genome Project Patentierung Gentechnik
Biowissenschaftlich recherchieren
 Biowissenschaftlich recherchieren Uber den Einsatz von Datenbanken und anderen Ressourcen der Bioinformatik Nicola Gaedeke Birkhauser Basel Boston Berlin Inhaltsverzeichnis Vorwort xi 1 Die Informationssucheim
Biowissenschaftlich recherchieren Uber den Einsatz von Datenbanken und anderen Ressourcen der Bioinformatik Nicola Gaedeke Birkhauser Basel Boston Berlin Inhaltsverzeichnis Vorwort xi 1 Die Informationssucheim
Pathologie und Prädiktion - neue Aspekte. Prof. Dr. med. C. Wickenhauser Institut für Pathologie
 Pathologie und Prädiktion - neue Aspekte Paradigmenwechsel in der Pathologie -Pathologe zentraler Lotse bei der individuellen Therapieentscheidung -Gewebeuntersuchung nicht nur aus diagnostischen sondern
Pathologie und Prädiktion - neue Aspekte Paradigmenwechsel in der Pathologie -Pathologe zentraler Lotse bei der individuellen Therapieentscheidung -Gewebeuntersuchung nicht nur aus diagnostischen sondern
BIOINFORMATIK UEBUNGEN MOLZEB SS2014
 BIOINFORMATIK UEBUNGEN MOLZEB SS2014 Dietmar Rieder icbi.at/courses/bioinformatics_lfu.html Organisatorisches Termine Übungsziele Kennlernen biologischer Datenbanken (NCBI, ) Arbeiten mit Protein und DNA/RNA
BIOINFORMATIK UEBUNGEN MOLZEB SS2014 Dietmar Rieder icbi.at/courses/bioinformatics_lfu.html Organisatorisches Termine Übungsziele Kennlernen biologischer Datenbanken (NCBI, ) Arbeiten mit Protein und DNA/RNA
Algorithmen auf Sequenzen 12.04.2010
 Algorithmen auf Sequenzen 12.04.2010 Prof. Dr. Sven Rahmann 1 Team Prof. Dr. Sven Rahmann Dipl.-Inform Tobias Marschall (Skript) Zeit Mo 8:30-10; Übungen Mi 8:30-10 ca. alle 2 Wochen (Plan!) Ort OH14,
Algorithmen auf Sequenzen 12.04.2010 Prof. Dr. Sven Rahmann 1 Team Prof. Dr. Sven Rahmann Dipl.-Inform Tobias Marschall (Skript) Zeit Mo 8:30-10; Übungen Mi 8:30-10 ca. alle 2 Wochen (Plan!) Ort OH14,
Größenvergleich zwischen verschiedenen Wirkstoffen
 Acetylsalicylsäure (ASS) Insulin monoklonaler Antikörper (Abbildung: vfa) 21 Atome 788 Atome ca. 20.000 Atome Größenvergleich zwischen verschiedenen Wirkstoffen Wichtige gentechnisch hergestellte Biopharmazeutika
Acetylsalicylsäure (ASS) Insulin monoklonaler Antikörper (Abbildung: vfa) 21 Atome 788 Atome ca. 20.000 Atome Größenvergleich zwischen verschiedenen Wirkstoffen Wichtige gentechnisch hergestellte Biopharmazeutika
Grundsätze der Patentierung technischer und biotechnischer Erfindungen
 Grundsätze der Patentierung technischer und biotechnischer Erfindungen Dr. Christof Friedrich 1. Allgemeines 2. Patentfähige Erfindungen 3. Patentprüfung 4. Biotechnologie 1 Was ist ein Patent? Vertrag
Grundsätze der Patentierung technischer und biotechnischer Erfindungen Dr. Christof Friedrich 1. Allgemeines 2. Patentfähige Erfindungen 3. Patentprüfung 4. Biotechnologie 1 Was ist ein Patent? Vertrag
Klonierung von S2P Rolle der M19-Zellen. POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel
 Klonierung von S2P Rolle der M19-Zellen POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel Inhalt 1. Was ist eine humane genomische DNA-Bank? 2. Unterschied zwischen cdna-bank und genomischer DNA-Bank?
Klonierung von S2P Rolle der M19-Zellen POL-Seminar der Biochemie II 13.02.2007 Sebastian Gabriel Inhalt 1. Was ist eine humane genomische DNA-Bank? 2. Unterschied zwischen cdna-bank und genomischer DNA-Bank?
Proseminarvortrag. Markov-Ketten in der Biologie (Anwendungen)
 Proseminarvortrag Markov-Ketten in der Biologie (Anwendungen) von Peter Drössler 20.01.2010 2 Markov-Ketten in der Biologie (Peter Drössler, KIT 2010) Inhalt 1. Das Wright-Fisher Modell... 3 1.1. Notwendige
Proseminarvortrag Markov-Ketten in der Biologie (Anwendungen) von Peter Drössler 20.01.2010 2 Markov-Ketten in der Biologie (Peter Drössler, KIT 2010) Inhalt 1. Das Wright-Fisher Modell... 3 1.1. Notwendige
Spleissen Dezember 2009 Elmar Schiebel, ZMBH
 Spleissen Dezember 2009 Elmar Schiebel, ZMBH Bis 1970s: Eine Gen besteht aus einem Stück doppelsträngiger DNA. Dieses einfache Bild wurde 1977 durch die Entdeckung von Richard J. Roberts (Cold Spring Harbor
Spleissen Dezember 2009 Elmar Schiebel, ZMBH Bis 1970s: Eine Gen besteht aus einem Stück doppelsträngiger DNA. Dieses einfache Bild wurde 1977 durch die Entdeckung von Richard J. Roberts (Cold Spring Harbor
A- Zugabe von 180µl Pufferlösung und Proteinase K, Inkubation bei 56 C. B- Zugabe von 200µl einer zweiten Pufferlösung, Inkubation bei 70 C
 3 Methoden 3.1 Extraktion der DNA aus den Paraffinschnitten 3.1.1 Extraktions-Kit Das QIAamp DNA Mini Kit- System beruht auf dem Prinzip der Auflösung der Eiweiße mit Proteinase K, DNA Bindung an eine
3 Methoden 3.1 Extraktion der DNA aus den Paraffinschnitten 3.1.1 Extraktions-Kit Das QIAamp DNA Mini Kit- System beruht auf dem Prinzip der Auflösung der Eiweiße mit Proteinase K, DNA Bindung an eine
Inhalt 1 Modellorganismen
 Inhalt 1 Modellorganismen....................................... 1 1.1 Escherichia coli....................................... 1 1.1.1 Historisches...................................... 3 1.1.2 Lebenszyklus.....................................
Inhalt 1 Modellorganismen....................................... 1 1.1 Escherichia coli....................................... 1 1.1.1 Historisches...................................... 3 1.1.2 Lebenszyklus.....................................
molekularen Rinderzucht
 Möglichkeiten der molekularen Rinderzucht Johann Sölkner Gliederung Einleitung Molekulare Marker Suche nach wichtigen Genen Molekulare Zuchtwertschätzung Auswirkung auf Zuchtprogramme Versprechen der Molekulargenetiker
Möglichkeiten der molekularen Rinderzucht Johann Sölkner Gliederung Einleitung Molekulare Marker Suche nach wichtigen Genen Molekulare Zuchtwertschätzung Auswirkung auf Zuchtprogramme Versprechen der Molekulargenetiker
Übungsblatt: Protein interaction networks. Ulf Leser and Samira Jaeger
 Übungsblatt: Protein interaction networks Ulf Leser and Samira Jaeger Aufgabe 1 Netzwerkzentralität (6P) In der Vorlesung haben Degree Centrality besprochen. Finde drei weitere etablierte Zentralitätsmaße
Übungsblatt: Protein interaction networks Ulf Leser and Samira Jaeger Aufgabe 1 Netzwerkzentralität (6P) In der Vorlesung haben Degree Centrality besprochen. Finde drei weitere etablierte Zentralitätsmaße
Funktionelle Genomik. praktische Anwendungen
 Funktionelle Genomik praktische Anwendungen Schmelzpunkt der DNA Einzelsträngige DNA absorbiert UV-Licht effektiver SYBR Green fluoresziert nur wenn es an doppelsträngiger DNA bindet Fluoreszenz erhöht
Funktionelle Genomik praktische Anwendungen Schmelzpunkt der DNA Einzelsträngige DNA absorbiert UV-Licht effektiver SYBR Green fluoresziert nur wenn es an doppelsträngiger DNA bindet Fluoreszenz erhöht
Genetik - The Human Genome Project. Überblick über die Genetik. Die gesamte Erbinformation eines Menschen befindet sich in jedem Zellkern
 Genetik - The Human Genome Project Überblick über die Genetik Die gesamte Erbinformation eines Menschen befindet sich in jedem Zellkern seines Körpers. 1 2 Im Organismus müsssen nun ständig Enzyme u. a.
Genetik - The Human Genome Project Überblick über die Genetik Die gesamte Erbinformation eines Menschen befindet sich in jedem Zellkern seines Körpers. 1 2 Im Organismus müsssen nun ständig Enzyme u. a.
Das Human-Genom und seine sich abzeichnende Dynamik
 Das Human-Genom und seine sich abzeichnende Dynamik Matthias Platzer Genomanalyse Leibniz Institut für Altersforschung - Fritz-Lipmann Institut (FLI) Humangenom - Sequenzierung 1. Methode 2. Ergebnisse
Das Human-Genom und seine sich abzeichnende Dynamik Matthias Platzer Genomanalyse Leibniz Institut für Altersforschung - Fritz-Lipmann Institut (FLI) Humangenom - Sequenzierung 1. Methode 2. Ergebnisse
MOL.504 Analyse von DNA- und Proteinsequenzen
 MOL.504 Analyse von DNA- und Proteinsequenzen Vorbereitung: Start des Serial Cloners ( unter Laufwerk K: im Ordner Win_SerialCloner2-5 Programm direkt im Ordner starten) K:\Win_SerialCloner2-5 (oder 2-6
MOL.504 Analyse von DNA- und Proteinsequenzen Vorbereitung: Start des Serial Cloners ( unter Laufwerk K: im Ordner Win_SerialCloner2-5 Programm direkt im Ordner starten) K:\Win_SerialCloner2-5 (oder 2-6
Factsheet Gebärmutterhalskrebs
 Factsheet Gebärmutterhalskrebs Verbreitung und Neuerkrankungen Ursachen und Risikofaktoren Therapie Primärprävention Sekundärprävention 1 Verbreitung und Neuerkrankungen Gebärmutterhalskrebs (in der Fachsprache
Factsheet Gebärmutterhalskrebs Verbreitung und Neuerkrankungen Ursachen und Risikofaktoren Therapie Primärprävention Sekundärprävention 1 Verbreitung und Neuerkrankungen Gebärmutterhalskrebs (in der Fachsprache
ZytoFast HPV High-Risk (HR) Types Probe (Digoxigenin
 ZytoFast HPV High-Risk (HR) Types Probe (Digoxigenin Digoxigenin-markiert markiert) T-1140-400 40 (0,4 ml) Zum Nachweis von Human Papilloma Virus (HPV) Typ 16/18/31/33/35/39/45/51/52/56/58/59/66/68/82
ZytoFast HPV High-Risk (HR) Types Probe (Digoxigenin Digoxigenin-markiert markiert) T-1140-400 40 (0,4 ml) Zum Nachweis von Human Papilloma Virus (HPV) Typ 16/18/31/33/35/39/45/51/52/56/58/59/66/68/82
Was kommt nach dem Human-GenomProjekt? Stand der Forschung und ethische Fragen
 Was kommt nach dem Human-GenomProjekt? Stand der Forschung und ethische Fragen Humangenom Größe 150 m 3.000.000.000 Nukleotide 3000 x 1000 x 1000 Bücher Seiten Buchstaben 1953 2003 Watson, J.D., and F.H.C.Crick.
Was kommt nach dem Human-GenomProjekt? Stand der Forschung und ethische Fragen Humangenom Größe 150 m 3.000.000.000 Nukleotide 3000 x 1000 x 1000 Bücher Seiten Buchstaben 1953 2003 Watson, J.D., and F.H.C.Crick.
MiniMed 11.05.2006 1
 MiniMed 11.05.2006 1 neue Wege in der Medizin - die Impfung gegen Gebärmutterhalskrebs Dr. Heide Lingard Medizinische Universität t Wien Abteilung Allgemein- & Familienmedizin worum geht es? Erstmals wird
MiniMed 11.05.2006 1 neue Wege in der Medizin - die Impfung gegen Gebärmutterhalskrebs Dr. Heide Lingard Medizinische Universität t Wien Abteilung Allgemein- & Familienmedizin worum geht es? Erstmals wird
ÜBERSICHTSRASTER ZU DEN UNTERRICHTSVORHABEN IN BIOLOGIE IN DER EINFÜHRUNGSPHASE (EP)
 ÜBERSICHTSRASTER ZU DEN UNTERRICHTSVORHABEN IN BIOLOGIE IN DER EINFÜHRUNGSPHASE (EP) THEMA Kein Leben ohne Zelle I KONTEXT Wie sind Zellen aufgebaut und organisiert? INHALTSFELD IF 1 (Biologie der Zelle)
ÜBERSICHTSRASTER ZU DEN UNTERRICHTSVORHABEN IN BIOLOGIE IN DER EINFÜHRUNGSPHASE (EP) THEMA Kein Leben ohne Zelle I KONTEXT Wie sind Zellen aufgebaut und organisiert? INHALTSFELD IF 1 (Biologie der Zelle)
Amplifikation von EGFR beim Lungen- (Adenokarzinom) oder Magenkarzinom
 Leistungsspektrum Alle Untersuchungen können grundsätzlich an formalinfixierten paraffineingebetteten Gewebeproben, Schnittpräparaten oder EDTA-Blut durchgeführt werden. Auflistung nach Untersuchungen
Leistungsspektrum Alle Untersuchungen können grundsätzlich an formalinfixierten paraffineingebetteten Gewebeproben, Schnittpräparaten oder EDTA-Blut durchgeführt werden. Auflistung nach Untersuchungen
Anlage zur Akkreditierungsurkunde D-PL-13372-01-00 nach DIN EN ISO/IEC 17025:2005
 Deutsche Akkreditierungsstelle GmbH Anlage zur Akkreditierungsurkunde D-PL-13372-01-00 nach DIN EN ISO/IEC 17025:2005 Gültigkeitsdauer: 26.06.2015 bis 25.03.2017 Ausstellungsdatum: 26.06.2015 Urkundeninhaber:
Deutsche Akkreditierungsstelle GmbH Anlage zur Akkreditierungsurkunde D-PL-13372-01-00 nach DIN EN ISO/IEC 17025:2005 Gültigkeitsdauer: 26.06.2015 bis 25.03.2017 Ausstellungsdatum: 26.06.2015 Urkundeninhaber:
Krebstherapie durch Aktivierung des Immunsystems
 Powered by Seiten-Adresse: https://www.gesundheitsindustriebw.de/de/fachbeitrag/aktuell/krebstherapie-durchaktivierung-des-immunsystems/ Krebstherapie durch Aktivierung des Immunsystems Schutzimpfungen,
Powered by Seiten-Adresse: https://www.gesundheitsindustriebw.de/de/fachbeitrag/aktuell/krebstherapie-durchaktivierung-des-immunsystems/ Krebstherapie durch Aktivierung des Immunsystems Schutzimpfungen,
Ersatz für geschädigte Zellen Ansätze der regenerativen Medizin
 CAMPUS INNENSTADT Diabetes Zentrum Ersatz für geschädigte Zellen Ansätze der regenerativen Medizin Jochen Seißler Diabeteszentrum Ludwig-Maximilians-Universität München Intensivierte Insulintherapie: enges
CAMPUS INNENSTADT Diabetes Zentrum Ersatz für geschädigte Zellen Ansätze der regenerativen Medizin Jochen Seißler Diabeteszentrum Ludwig-Maximilians-Universität München Intensivierte Insulintherapie: enges
Studiengang Informatik der FH Gießen-Friedberg. Sequenz-Alignment. Jan Schäfer. WS 2006/07 Betreuer: Prof. Dr. Klaus Quibeldey-Cirkel
 Studiengang Informatik der FH Gießen-Friedberg Sequenz-Alignment Jan Schäfer WS 2006/07 Betreuer: Prof. Dr. Klaus Quibeldey-Cirkel Überblick Einführung Grundlagen Wann ist das Merkmal der Ähnlichkeit erfüllt?
Studiengang Informatik der FH Gießen-Friedberg Sequenz-Alignment Jan Schäfer WS 2006/07 Betreuer: Prof. Dr. Klaus Quibeldey-Cirkel Überblick Einführung Grundlagen Wann ist das Merkmal der Ähnlichkeit erfüllt?
drawbar eye series 2010
 drawbar eye series 2010 directive 94/20/EG / class S DIN 74054-40A / material St52-3 (no. 1.0570) / with bush 40 mm parameters for centre-axle trailer s ṣhaft cross section order no H x B mm length A mm
drawbar eye series 2010 directive 94/20/EG / class S DIN 74054-40A / material St52-3 (no. 1.0570) / with bush 40 mm parameters for centre-axle trailer s ṣhaft cross section order no H x B mm length A mm
UCLA UCLA. Welche Tumoren/Patientinnen sind wirklich endokrin resistent? Was bedeutet es für die Klinik? Peter A. Fasching
 Welche Tumoren/Patientinnen sind wirklich endokrin resistent? Was bedeutet es für die Klinik? Peter A. Fasching UCLA David Geffen School of Medicine Dep. Hem/Onc UCLA Endokrine Resistenz wo müssen wir
Welche Tumoren/Patientinnen sind wirklich endokrin resistent? Was bedeutet es für die Klinik? Peter A. Fasching UCLA David Geffen School of Medicine Dep. Hem/Onc UCLA Endokrine Resistenz wo müssen wir
Auswertung PCR. Übersicht Nachweise mittels PCR. 1. Beta-Globin
 Übersicht Nachweise mittels PCR Lfd.-Nr. Nachweis von: Elektrophorese/Photometrie/ Luminometrie/ Fragmentanalyse/Sequenzierung/ Restriktionsanalyse 1. Beta-Globin 267 bp (zum Nachweis der DNA- Qualität)
Übersicht Nachweise mittels PCR Lfd.-Nr. Nachweis von: Elektrophorese/Photometrie/ Luminometrie/ Fragmentanalyse/Sequenzierung/ Restriktionsanalyse 1. Beta-Globin 267 bp (zum Nachweis der DNA- Qualität)
QIAGEN erwirbt Rechte an genetischen Biomarkern für Hirntumore, Lungen- und andere Krebsarten
 QIAGEN erwirbt Rechte an genetischen Biomarkern für Hirntumore, Lungen- und andere Krebsarten Hilden (10. Januar 2012) - QIAGEN hat von zwei US-amerikanischen Biotechnologieunternehmen weltweit exklusive
QIAGEN erwirbt Rechte an genetischen Biomarkern für Hirntumore, Lungen- und andere Krebsarten Hilden (10. Januar 2012) - QIAGEN hat von zwei US-amerikanischen Biotechnologieunternehmen weltweit exklusive
Bioinformatik an der FH Bingen
 Bioinformatik an der FH Bingen Prof. Dr. Antje Krause 05.11.2010 Wie alles begann... 1955 erste Proteinsequenz (nach 12 Jahren Arbeit) veröffentlicht (Insulin vom Rind) Frederick Sanger MALWTRLRPLLALLALWPPPPA
Bioinformatik an der FH Bingen Prof. Dr. Antje Krause 05.11.2010 Wie alles begann... 1955 erste Proteinsequenz (nach 12 Jahren Arbeit) veröffentlicht (Insulin vom Rind) Frederick Sanger MALWTRLRPLLALLALWPPPPA
Exkurs 4: Oligonucleotide als Antisense Wirkstoffe
 Exkurs 4: ligonucleotide als Antisense Wirkstoffe Pharmazeutische Biochemie Antisense Wirkstoffe am Markt Fomivirsen (INN) Handelsname Vitravene Einsatz: Lokale Behandlung von Zytomegalie-Virus Infektionen
Exkurs 4: ligonucleotide als Antisense Wirkstoffe Pharmazeutische Biochemie Antisense Wirkstoffe am Markt Fomivirsen (INN) Handelsname Vitravene Einsatz: Lokale Behandlung von Zytomegalie-Virus Infektionen
Medizinische Fakultät Auswertestrategien von Microarrays Einführung
 Medizinische Fakultät Auswertestrategien von Microarrays Einführung PD Dr. Knut Krohn IZKF Leipzig Dr. Markus Eszlinger Med. Klinik III Forschungslabor DNA RNA Hintergrund Charakteristisches Muster der
Medizinische Fakultät Auswertestrategien von Microarrays Einführung PD Dr. Knut Krohn IZKF Leipzig Dr. Markus Eszlinger Med. Klinik III Forschungslabor DNA RNA Hintergrund Charakteristisches Muster der
Aufbau und Funktion des Genoms: Von der Genstruktur zur Funktion
 Assoc. Prof. PD Mag. Dr. Aufbau und Funktion des Genoms: Von der Genstruktur zur Funktion Wien, 2013 Währinger Straße 10, A-1090 Wien helmut.dolznig@meduniwien.ac.at www.meduniwien.ac.at/medizinische-genetik
Assoc. Prof. PD Mag. Dr. Aufbau und Funktion des Genoms: Von der Genstruktur zur Funktion Wien, 2013 Währinger Straße 10, A-1090 Wien helmut.dolznig@meduniwien.ac.at www.meduniwien.ac.at/medizinische-genetik
Die HPV-Impfung gegen Gebärmutterhalskrebs. Eine gesundheitspolitische Fragwürdigkeit.
 Studien / Statistiken / Medienberichte allgemein 16 / 5 / 1 HPV-Impfung und gesundheitspolitische Fragwürdigkeit Die HPV-Impfung gegen Gebärmutterhalskrebs. Eine gesundheitspolitische Fragwürdigkeit. 22.
Studien / Statistiken / Medienberichte allgemein 16 / 5 / 1 HPV-Impfung und gesundheitspolitische Fragwürdigkeit Die HPV-Impfung gegen Gebärmutterhalskrebs. Eine gesundheitspolitische Fragwürdigkeit. 22.
Hämatologische und onkologische Fachgesellschaften gehen gestärkt aus ihrer Jahrestagung
 Gemeinsame Jahrestagung 2009 der DGHO, ÖGHO, SGMO und SGH+SSH, Heidelberg / Mannheim, 2. bis 6. Oktober 2009 Hämatologische und onkologische Fachgesellschaften gehen gestärkt aus ihrer Jahrestagung Mannheim
Gemeinsame Jahrestagung 2009 der DGHO, ÖGHO, SGMO und SGH+SSH, Heidelberg / Mannheim, 2. bis 6. Oktober 2009 Hämatologische und onkologische Fachgesellschaften gehen gestärkt aus ihrer Jahrestagung Mannheim
DAS METABOLOM: ERNÄHRUNGSSTATUS, METABOLISMUS, METABOLITEN
 DAS METABOLOM: ERNÄHRUNGSSTATUS, METABOLISMUS, METABOLITEN Das Metabolom Extrinsiche Faktoren Ernährung (Nährstoffe und nicht nutritive Lebensmittelinhaltsstoffe) Arzneimittel Physische Aktivität Darmflora
DAS METABOLOM: ERNÄHRUNGSSTATUS, METABOLISMUS, METABOLITEN Das Metabolom Extrinsiche Faktoren Ernährung (Nährstoffe und nicht nutritive Lebensmittelinhaltsstoffe) Arzneimittel Physische Aktivität Darmflora
Inhaltsverzeichnis... I. Abbildungs- und Tabellenverzeichnis... VI. Abkürzungsverzeichnis... IX. 1 Einleitung... 1
 I... I Abbildungs- und Tabellenverzeichnis... VI Abkürzungsverzeichnis... IX 1 Einleitung... 1 1.1 Untersuchte uro-rektale Fehlbildungen... 1 1.1.1 Blasenekstrophie-Epispadie-Komplex (BEEK)... 1 1.1.1.1
I... I Abbildungs- und Tabellenverzeichnis... VI Abkürzungsverzeichnis... IX 1 Einleitung... 1 1.1 Untersuchte uro-rektale Fehlbildungen... 1 1.1.1 Blasenekstrophie-Epispadie-Komplex (BEEK)... 1 1.1.1.1
Brustkrebs aktuell - OSP am Was ist eigentlich die Aufgabe des Pathologen in Diagnostik und Therapie des Mammakarzinoms?
 Brustkrebs aktuell - OSP am 21.10.2015 Was ist eigentlich die Aufgabe des Pathologen in Diagnostik und Therapie des Mammakarzinoms? Prof. Dr. German Ott, Institut für Pathologie Robert-Bosch-Krankenhaus
Brustkrebs aktuell - OSP am 21.10.2015 Was ist eigentlich die Aufgabe des Pathologen in Diagnostik und Therapie des Mammakarzinoms? Prof. Dr. German Ott, Institut für Pathologie Robert-Bosch-Krankenhaus
