Struktur in der Bioinformatik
|
|
|
- Arwed Armbruster
- vor 6 Jahren
- Abrufe
Transkript
1 Struktur in der Bioinformatik Rolf Backofen Lehrstuhl für Bioinformatik Institut für Informatik FS Jena Überblick Einführung nwendungsbeispiel: Selenoproteine Proteinfaltung Protein Docking c R. Backofen 1
2 Funktion und Programm Fakultätsfunktion f(0) := 1 f(i + 1) := f(i) (i + 1) Programm: int n,f,i; main (i/nt argc, char argv[]) { n = atoi(argv[1]); f=1; for (i=0;i<n;i++) f = f(i+1); printf("%i\n",f); } c R. Backofen 2-a
3 457f464c d001a c c f f f e c c c080400a a c2f62696c2f2d64696c756e2e786f73322e e a d ba e e004d f f00675f 6f6d5f6e f74005f696c e2e6f e f00645f f d615f656e696f f f5f4f f6e f006c5f62695f f74616d6e695f00725f f d615f656e696f c f 302e d c e500e800005b00c381125f0000 bb e8057d22f7fbf6890be80001e80001b600005d8b89fc5dec00c ff952c ff ff e900ffe0ffff25ff e900 ffd0ffff25ff953c e900ffc0ffff25ff e900ffb0ffff25ff e900ffa0ffff ed31895e83e1f8e e00804 c a3e8fffff4ff e5103d febf689508d89040c b08ff00a1d0950c b8e c0850a e808ff4affff05c ec89c35d8d9026b e55dec89c3 8df627bc b8e c R. Backofen 2-b
4 Vergleich: menschl. hromosom 22 (33.4 Mio Basenpaare) GTTGTGTGGTTGGGTGTGGTTGGGTTTTTTGGTTGGTGGG TGTGTTTGGGTGGTTGGGGGGTTGTTGGTTTTTGTTTTTGTT TTTGTGTGGTGGGTTGTGGTGGGTGGGGGTTTTGTTTTTTTTT GGTTTTTTTTTTTTTTGGGGGGGTTTTTTTTTTTGGTGTTTGTGT TGTTTTTTTTTTGTTTGGGGTTTTTTTTTTGTTGGTTTGG TTTGTTTTGGTTGTGGTTTTGTGTTTTTTTTTTTGGTGTG TGTTTTGTGGTGGGGGGTTTTGTTTTTTTTTTGGGT TTTTTTTTTTTTGGGTGTGTGGGTTTTGTGTGGGTGTGGTTGTG GTGGTTGTTTTTGGTTTTTGTTGTGTTTTTGGGTTTTTTG GGGTTGGTGTTTTTTTGTGTTTTGGTGGTTTTTTTTTTTTGTTGGG TTTTTGGGTGGTTGGGGGTGTTTGGTTGTGGGGTT TGTTTTGTTGTTGGGTGTTGTGTTGTGGGGGGGTTGTTTGGGGTG GGTTTGGTGGTGTGGTGTGGTGTGTTTTTTGTTGGTGTGTTGT TTTTTGTGGGGTGGGGGTGTGTTTGGGTTTTTGTGTT TTGTTTGGGGTTTTTGTGTTGGTGTGGTTTTTGTT TTTTTGGGTTTTTTTTTTTGGTTGTGTGTTGTGTGGTGGTTGGGT GTTTGGTTTTGTTGTTTTTGGTTTTGGTGTTGG TTGTGTTGGGGGGGGTGGTTTTTTTTGTTTGT TTTTGGTGTTGTTTGTGGTTTTGGGGGTTGTTTGTTG GTTTGGGTGTGGGGGGGGTTTGGTTGTTTTGTTTTTTGTTGGG GTTTGTTTTGTTTGGTTTTTTGTTTTTTTGTGTTGGGGTT TTGTTTTTGTTTTTTTGTTTTTTTTGTTTTTT TTGTGGGTTGTTTTTTTGTGGGTTTGTGGTGTG TTTTTGTTTGTTTGTTGGTGGTGGGTGGTTGTGTTG TTTGGGGGTGGGGGGTGTTGGGTGGGTTGGTGGTGGTGGTT TTTTGGTTGGTGGTGGG... c R. Backofen 2-c
5 Funktion Funktion wird verstanden aus 3-dimensionaler Struktur Sekundärstruktur Organisationsstruktur c R. Backofen 2-d
6 Bioinformatik: Essentiell für Biologische Forschung Beispiel Genom Genom Sequenz GTTGTGTGGTTGGGTGTGGTTGGGTTTTTTGGTT GGTGGGTGTGTTTGGGTGGTTGGGGGGTTGTTGGTTTTT GTTTTTGTTTTTGTGTGGTGGGTTGTGGTGGGTGGGGGT TTTGTTTTTTTTTGGTTTTTTTTTTTTTTGGGGGGGTTT TTTTTTTTGGTGTTTGTGTTGTTTTTTTTTTGTTTGGGGT TTTTTTTTTGTTGGTTTGGTTTGTTTTGGTTGTGGT TTTGTGTTTTTTTTTTTGGTGTGTGTTTTG TGGTGGGGGGTTTTGTTTTTTTTTTGGGTTTTTTTTTTT TTGGGTGTGTGGGTTTTGTGTGGGTGTGGTTGTGGTGG TTGTTTTTGGTTTTTGTTGTGTTTTTGGGTTTTTTG GGGTTGGTGTTTTTTTGTGTTTTGGTGGTTTTTTTTTTTTG TTGGGTTTTTGGGTGGTTGGGGGTGTTTGGTTGT GGGGTTTGTTTTGTTGTTGGGTGTTGTGTTGTGGGG GGGTTGTTTGGGGTGGGTTTGGTGGTGTGGTGTGGTGTGTT TTTTGTTGGTGTGTTGTTTTTTGTGGGGTGGGGG TGTGTTTGGGTTTTTGTGTTTTGTTTGGGGTT TTTGTGTTGGTGTGGTTTTTGTTTTTTTGGGTTTTTT Zerschneiden TTTTTGGTTGTGTGTTGTGTGGTGGTTGGGTGTTTGG TTTTGTTGTTTTTGGTTTTGGTGTTGGTT GTGTTGGGGGGGGTGGTTTTTTTTGTTTGT TTTTGGTGTTGTTTGTGGTTTTGGGGGTTGTTT GTTGGTTTGGGTGTGGGGGGGGTTTGGTTGTTTTGTTTTTTGT TGGGGTTTGTTTTGTTTGGTTTTTTGTTTTTT TGTGTTGGGGTTTTGTTTTTGTTTTTTT GTTTTTTTTGTTTTTTTTGTGGGTTGTTTTTTTG TGGGTTTGTGGTGTGTTTTTGTTTGTTTGTTG GTGGTGGGTGGTTGTGTTGTTTGGGGGTGGGGGGTGT TGGGTGGGTTGGTGGTGGTGGTTTTT Whole Shotgun Sequencing GT... G... TG... GG... Sequenzierung der Fragmente Überlagerung...GT G G TG... ber: lgorithmus biologische Wirklichkeit (Bsp. Repeats)... GGG GGGG... GGGG GGGG... c R. Backofen 3
7 Bioinformatik: Essentiell für Biologische Forschung Beispiel Genom Genom Sequenz GTTGTGTGGTTGGGTGTGGTTGGGTTTTTTGGTT GGTGGGTGTGTTTGGGTGGTTGGGGGGTTGTTGGTTTTT GTTTTTGTTTTTGTGTGGTGGGTTGTGGTGGGTGGGGGT TTTGTTTTTTTTTGGTTTTTTTTTTTTTTGGGGGGGTTT TTTTTTTTGGTGTTTGTGTTGTTTTTTTTTTGTTTGGGGT TTTTTTTTTGTTGGTTTGGTTTGTTTTGGTTGTGGT TTTGTGTTTTTTTTTTTGGTGTGTGTTTTG TGGTGGGGGGTTTTGTTTTTTTTTTGGGTTTTTTTTTTT TTGGGTGTGTGGGTTTTGTGTGGGTGTGGTTGTGGTGG TTGTTTTTGGTTTTTGTTGTGTTTTTGGGTTTTTTG GGGTTGGTGTTTTTTTGTGTTTTGGTGGTTTTTTTTTTTTG TTGGGTTTTTGGGTGGTTGGGGGTGTTTGGTTGT GGGGTTTGTTTTGTTGTTGGGTGTTGTGTTGTGGGG GGGTTGTTTGGGGTGGGTTTGGTGGTGTGGTGTGGTGTGTT TTTTGTTGGTGTGTTGTTTTTTGTGGGGTGGGGG TGTGTTTGGGTTTTTGTGTTTTGTTTGGGGTT TTTGTGTTGGTGTGGTTTTTGTTTTTTTGGGTTTTTT Zerschneiden TTTTTGGTTGTGTGTTGTGTGGTGGTTGGGTGTTTGG TTTTGTTGTTTTTGGTTTTGGTGTTGGTT GTGTTGGGGGGGGTGGTTTTTTTTGTTTGT TTTTGGTGTTGTTTGTGGTTTTGGGGGTTGTTT GTTGGTTTGGGTGTGGGGGGGGTTTGGTTGTTTTGTTTTTTGT TGGGGTTTGTTTTGTTTGGTTTTTTGTTTTTT TGTGTTGGGGTTTTGTTTTTGTTTTTTT GTTTTTTTTGTTTTTTTTGTGGGTTGTTTTTTTG TGGGTTTGTGGTGTGTTTTTGTTTGTTTGTTG GTGGTGGGTGGTTGTGTTGTTTGGGGGTGGGGGGTGT TGGGTGGGTTGGTGGTGGTGGTTTTT Whole Shotgun Sequencing GT... G... TG... GG... Sequenzierung der Fragmente Überlagerung...GT G G TG... ber: lgorithmus biologische Wirklichkeit (Bsp. Repeats)... GGG GGGG... GGGG GGGG... c R. Backofen 3
8 Zentrales Dogma DNS: lineare Kette von Nukleotiden {,,G,T} RNS: lineare Kette von Nukleotiden {,,G,} Proteine: lineare Kette von minosäuren (20 versch.) Informationsfluß in der Biologie: DN RN Protein c R. Backofen 4
9 3 Hauptbereiche der Bioinformatik auf zentrales Dogma bezogen: Sequenz, Struktur und Funktion von Proteinen Datenbezogen Speicherung (Repräsentation) und Suche Datenanalyse, Data mining exponentielles Wachstum der Daten Simulation von biologischen Prozessen Proteinfaltung, Metabolische Pfade E-ell c R. Backofen 5
10 Weiterer Inhalt nwendungsbeispiel: Selenoproteine seltene, aber wichtige minosäure Selenocystein Translation strukturabhängig relevante Bioinformatikprobleme Proteinfaltung Problemdefinition und Lösungansätze Proteinfaltung im Kontext Proteindocking c R. Backofen 6
11 Translation von Proteinen DN mrn Protein n His genetischer ode: 20 minosäuren alle odons belegt odon G Phe Ser Tyr ys Phe Ser Tyr ys Leu Ser Stop Stop Leu Ser Stop Trp G Leu Pro His rg STOP-odon: mrn Ribosom G STOP c R. Backofen 7
12 Selenocystein (Sec) Selenocystein (Sec): zusätzliche, 21te minosäure! in allen Domänen kodiert durch STOP-codon G (Overloading!) Selenoproteine: Proteine mit Selenocystein (Sec) wichtige Funktion (auch beim Menschen) Schutz vor oxidativen Streß, Selendiät Translation: erfordert SEIS-Element (= Sec Insertion Sequence) SEIS = Sequenz mit hairpin-artiger Struktur SEIS G c R. Backofen 8
13 Problem 1: DN und Proteinsequenz Gegeben DN Welche Proteinsequenz? GGG GGGGG RN-Sekundärstruktur: welche Basenpaarungen (, G)? dynamisches Programmierverfahren O(n 3 ). Bsp.: Maximale nzahl von Basenpaarung für a = a 1... a n Rekursionsgleichung für Paarungen von a i... a j : #-Paare(i + 1, j 1) + 1 falls (a i, a j ) paart #-Paare(i + 1, j) #-Paare(i, j) = max #-Paare(i, j 1) { } #-Paare(i, k) + #-Paare(k + 1, j) ktuelles Forschungsproblem: Pseudoknoten max i<k<j c R. Backofen 9
14 Problem 1: DN und Proteinsequenz Gegeben DN Welche Proteinsequenz? GGG GGGGG RN-Sekundärstruktur: welche Basenpaarungen (, G)? dynamisches Programmierverfahren O(n 3 ). Bsp.: Maximale nzahl von Basenpaarung für a = a 1... a n Rekursionsgleichung für Paarungen von a i... a j : #-Paare(i + 1, j 1) + 1 falls (a i, a j ) paart #-Paare(i + 1, j) #-Paare(i, j) = max #-Paare(i, j 1) { } #-Paare(i, k) + #-Paare(k + 1, j) ktuelles Forschungsproblem: Pseudoknoten max i<k<j c R. Backofen 9
15 Problem 1: DN und Proteinsequenz Gegeben DN Welche Proteinsequenz? GGG GGGGG RN-Sekundärstruktur: welche Basenpaarungen (, G)? dynamisches Programmierverfahren O(n 3 ). Bsp.: Maximale nzahl von Basenpaarung für a = a 1... a n Rekursionsgleichung für Paarungen von a i... a j : #-Paare(i + 1, j 1) + 1 falls (a i, a j ) paart #-Paare(i + 1, j) #-Paare(i, j) = max #-Paare(i, j 1) { } #-Paare(i, k) + #-Paare(k + 1, j) ktuelles Forschungsproblem: Pseudoknoten max i<k<j c R. Backofen 9
16 Problem 1: DN und Proteinsequenz Gegeben DN Welche Proteinsequenz? GGG GGGGG RN-Sekundärstruktur: welche Basenpaarungen (, G)? dynamisches Programmierverfahren O(n 3 ). Bsp.: Maximale nzahl von Basenpaarung für a = a 1... a n Rekursionsgleichung für Paarungen von a i... a j : #-Paare(i + 1, j 1) + 1 falls (a i, a j ) paart #-Paare(i + 1, j) #-Paare(i, j) = max #-Paare(i, j 1) { } #-Paare(i, k) + #-Paare(k + 1, j) ktuelles Forschungsproblem: Pseudoknoten max i<k<j c R. Backofen 9
17 Problem 2: harakterisierung von SEIS-Elementen SEIS-Element erlaubt Variation, Suche nach Sequenz/Strukturmuster notwendig, um Mechanismus aufzuklären. ber: nur Sequenzen bekannt, Struktur vermutet nsatz: Strukturen aus Strukturvorhersage Bestimmung der Konsensus-Struktur Sequenzalignment aus Konsensus-Struktur Sequenzalignment und Konsensus-Struktur consensus structure s 1 G G s 2 /G s 3 s 4 G G c R. Backofen 10
18 Problem 2: harakterisierung von SEIS-Elementen SEIS-Element erlaubt Variation, Suche nach Sequenz/Strukturmuster notwendig, um Mechanismus aufzuklären. ber: nur Sequenzen bekannt, Struktur vermutet nsatz: Strukturen aus Strukturvorhersage Bestimmung der Konsensus-Struktur Sequenzalignment aus Konsensus-Struktur Sequenzalignment und Konsensus-Struktur consensus structure s 1 G G s 2 /G s 3 s 4 G G c R. Backofen 10
19 Problem 2: harakterisierung von SEIS-Elementen SEIS-Element erlaubt Variation, Suche nach Sequenz/Strukturmuster notwendig, um Mechanismus aufzuklären. ber: nur Sequenzen bekannt, Struktur vermutet nsatz: Strukturen aus Strukturvorhersage Bestimmung der Konsensus-Struktur Sequenzalignment aus Konsensus-Struktur Sequenzalignment und Konsensus-Struktur consensus structure s 1 G G s 2 /G s 3 s 4 G G c R. Backofen 10
20 Problem 2: harakterisierung von SEIS-Elementen SEIS-Element erlaubt Variation, Suche nach Sequenz/Strukturmuster notwendig, um Mechanismus aufzuklären. ber: nur Sequenzen bekannt, Struktur vermutet nsatz: Strukturen aus Strukturvorhersage Bestimmung der Konsensus-Struktur Sequenzalignment aus Konsensus-Struktur Sequenzalignment und Konsensus-Struktur consensus structure s 1 G G s 2 /G s 3 s 4 G G c R. Backofen 10
21 Problem 2: harakterisierung von SEIS-Elementen SEIS-Element erlaubt Variation, Suche nach Sequenz/Strukturmuster notwendig, um Mechanismus aufzuklären. ber: nur Sequenzen bekannt, Struktur vermutet nsatz: Strukturen aus Strukturvorhersage Bestimmung der Konsensus-Struktur Sequenzalignment aus Konsensus-Struktur Sequenzalignment und Konsensus-Struktur consensus structure s 1 G G s 2 /G s 3 s 4 G G c R. Backofen 10
22 Problem 2: harakterisierung von SEIS-Elementen SEIS-Element erlaubt Variation, Suche nach Sequenz/Strukturmuster notwendig, um Mechanismus aufzuklären. ber: nur Sequenzen bekannt, Struktur vermutet nsatz: Strukturen aus Strukturvorhersage Bestimmung der Konsensus-Struktur Sequenzalignment aus Konsensus-Struktur Sequenzalignment und Konsensus-Struktur consensus structure s 1 G G s 2 /G s 3 s 4 G G c R. Backofen 10
23 Problem 2: harakterisierung von SEIS-Elementen SEIS-Element erlaubt Variation, Suche nach Sequenz/Strukturmuster notwendig, um Mechanismus aufzuklären. ber: nur Sequenzen bekannt, Struktur vermutet nsatz: Strukturen aus Strukturvorhersage Bestimmung der Konsensus-Struktur Sequenzalignment aus Konsensus-Struktur Sequenzalignment und Konsensus-Struktur consensus structure s 1 G G s 2 /G s 3 s 4 G G c R. Backofen 10
24 Problem 2: harakterisierung von SEIS-Elementen SEIS-Element erlaubt Variation, Suche nach Sequenz/Strukturmuster notwendig, um Mechanismus aufzuklären. ber: nur Sequenzen bekannt, Struktur vermutet nsatz: Strukturen aus Strukturvorhersage Bestimmung der Konsensus-Struktur Sequenzalignment aus Konsensus-Struktur Sequenzalignment und Konsensus-Struktur consensus structure s 1 G G s 2 /G s 3 s 4 G G c R. Backofen 10
25 Problem 2: harakterisierung von SEIS-Elementen SEIS-Element erlaubt Variation, Suche nach Sequenz/Strukturmuster notwendig, um Mechanismus aufzuklären. ber: nur Sequenzen bekannt, Struktur vermutet nsatz: Strukturen aus Strukturvorhersage Bestimmung der Konsensus-Struktur Sequenzalignment aus Konsensus-Struktur Sequenzalignment und Konsensus-Struktur consensus structure s 1 G G s 2 /G s 3 s 4 G G c R. Backofen 10
26 Problem 2: harakterisierung von SEIS-Elementen SEIS-Element erlaubt Variation, Suche nach Sequenz/Strukturmuster notwendig, um Mechanismus aufzuklären. ber: nur Sequenzen bekannt, Struktur vermutet nsatz: Strukturen aus Strukturvorhersage Bestimmung der Konsensus-Struktur Sequenzalignment aus Konsensus-Struktur Sequenzalignment und Konsensus-Struktur consensus structure s 1 G G s 2 /G s 3 s 4 G G c R. Backofen 10
27 Proteinfaltungsproblem Protein: lineare Sequenz von minosäuren GPSQPTYPG DDPVEDLI RFYDNLQQY LNVVTRHRY eindeutig = aber unbekannt native Konformation biochemische nsätze: aufwendig, schwierig Sequence/Structure Gap rotein Data Bank (PDB): Neueintragungen Strukturvorhersage: durch Faltungssimulation: nur kleine Moleküle als Suchproblem Vereinfachte Modelle 99 c R. Backofen 11
28 Proteinfaltungsproblem Protein: lineare Sequenz von minosäuren GPSQPTYPG DDPVEDLI RFYDNLQQY LNVVTRHRY eindeutig = aber unbekannt native Konformation biochemische nsätze: aufwendig, schwierig Sequence/Structure Gap rotein Data Bank (PDB): Neueintragungen Strukturvorhersage: durch Faltungssimulation: nur kleine Moleküle als Suchproblem Vereinfachte Modelle 99 c R. Backofen 11
29 Beispiel: Hierarchische nsätze zur Strukturvorhersage GPSQPTYPG DDPVEDLI RFYDNLQQY LNVVTRHRY Suche im Modell geringer uflösung Verfeinerung: biolog. Wissen, Faltungssimulation Modell geringer uflösung: Problem: bisher ad hoc Suchverfahren Bioinformatikmethoden c R. Backofen 12
30 Häufigste Modellklasse: Gittermodelle nur Backbone-Struktur, Position ˆ= Gitterpositionen kubisch: F: vereinfachte Energiefunktion: z.b. nur hydrophobe Kraft Komplexität: nzahl Konformation der Länge n: 4, 68 n native Konformation: NP-hart H c R. Backofen 13
31 Informatikansätze vollständige Enumeration: 4, 68 n Konformationen hauptsächlich: heuristische Methoden Monte arlo mit Simulated nnealing: local moves pivot moves : greedy: chain-growth Methode genetic algorithms klassische Optimierungsmethoden: branch-and-bound, ILP c R. Backofen 14
32 onstraint-basierte Strukturfaltung onstraint-programmierung: Branch-and-Bound + Propagierung Position i.te minos. p Position i.te minos. p Resultate: Threading auf 100er ore Seq. Länge Runtime S s S s S s S s c R. Backofen 15
33 onstraint-basierte Strukturfaltung onstraint-programmierung: Branch-and-Bound + Propagierung Position i.te minos. p Position i.te minos. p Resultate: Threading auf 100er ore Seq. Länge Runtime S s S s S s S s c R. Backofen 15
34 onstraint-basierte Strukturfaltung onstraint-programmierung: Branch-and-Bound + Propagierung Position i.te minos. p Position i.te minos. p Resultate: Threading auf 100er ore Seq. Länge Runtime S s S s S s S s c R. Backofen 15
35 Strukturvorhersage im Kontext Strukturvorhersage + homologie-basiertes Modellieren GPSQPTYPG DDPVEDLI RFYDNLQQY LNVVTRHRY, + PLEPEYPG DNTPEQM QYELRRY INMLTRPRY Proteindesign verwandtes Protein mit bekannter Struktur GPSQPTYPG DDPVEDLI RFYDNLQQY LNVVTRHRY Protein-Engineering: Modifikation bestehender Proteine c R. Backofen 16
36 Strukturvorhersage im Kontext Strukturvorhersage + homologie-basiertes Modellieren GPSQPTYPG DDPVEDLI RFYDNLQQY LNVVTRHRY, + PLEPEYPG DNTPEQM QYELRRY INMLTRPRY Proteindesign verwandtes Protein mit bekannter Struktur GPSQPTYPG DDPVEDLI RFYDNLQQY LNVVTRHRY Protein-Engineering: Modifikation bestehender Proteine c R. Backofen 16
37 Protein Docking 1:1-Docking Bestimme, ob und wie und B einen stabilen Komplex bilden B 1:n Docking Bestimme die Proteine in der Proteindatenbank PDB, die mit einen stabilen Komplex bilden? PDB = Probleme: komplexe Ähnlichkeit (Optimierierungsproblem, Branch-and-Bound) große Datenbanken Filterung der Einträge c R. Backofen 17
38 Similarity Ranking 3D Shape Histograms 1SER-B againts PDB c R. Backofen 18
39 Zusammenfassung Struktur in der Biologie: auf verschiedenen Ebenen 3-dimensionaler Struktur Sekundärstruktur Organisationsstruktur Sequence/Structure Gap Sequenz einfach, Strukturauflösung schwer entspr. Informatikproblem schwere Optimierungsprobleme ber: Funktion wird aus Struktur verstanden c R. Backofen 19
MOL.504 Analyse von DNA- und Proteinsequenzen
 MOL.504 Analyse von DNA- und Proteinsequenzen Kurs 1 Monika Oberer, Karl Gruber MOL.504 Modul-Übersicht Einführung, Datenbanken BLAST-Suche, Sequenzalignment Proteinstrukturen Virtuelles Klonieren Abschlusstest
MOL.504 Analyse von DNA- und Proteinsequenzen Kurs 1 Monika Oberer, Karl Gruber MOL.504 Modul-Übersicht Einführung, Datenbanken BLAST-Suche, Sequenzalignment Proteinstrukturen Virtuelles Klonieren Abschlusstest
Was ist Bioinformatik?
 9. Kurstag: Bioinformatik Der Begriff "Bioinformatik" wurde 1989 erstmals von D.R. Masys im JOURNAL OF RESEARCH OF THE NATIONAL INSTITUTE OF STANDARDS AND TECHNOLOGY erwähnt. Was ist Bioinformatik? Die
9. Kurstag: Bioinformatik Der Begriff "Bioinformatik" wurde 1989 erstmals von D.R. Masys im JOURNAL OF RESEARCH OF THE NATIONAL INSTITUTE OF STANDARDS AND TECHNOLOGY erwähnt. Was ist Bioinformatik? Die
MM Proteinmodelling. Michael Meyer. Vorlesung XVII
 Proteinmodelling Vorlesung XVII Proteinstrukturen Es besteht ein sehr großer Bedarf an Proteinstrukturen: Die Kenntnis der 3D-Struktur hat große Vorteile für das Design neuer Wirkstoffe. Experimentelle
Proteinmodelling Vorlesung XVII Proteinstrukturen Es besteht ein sehr großer Bedarf an Proteinstrukturen: Die Kenntnis der 3D-Struktur hat große Vorteile für das Design neuer Wirkstoffe. Experimentelle
Informationsvisualisierung
 Informationsvisualisierung Thema: 7. Visualisierung Biologischer Daten Dozent: Dr. Dirk Zeckzer zeckzer@informatik.uni-leipzig.de Sprechstunde: nach Vereinbarung Umfang: 2 Prüfungsfach: Modul Fortgeschrittene
Informationsvisualisierung Thema: 7. Visualisierung Biologischer Daten Dozent: Dr. Dirk Zeckzer zeckzer@informatik.uni-leipzig.de Sprechstunde: nach Vereinbarung Umfang: 2 Prüfungsfach: Modul Fortgeschrittene
1/10. Ihre Namen: Gruppe: Evolutionsbiologie 2, WS2015/2016: Bioinformatik - Übung 1
 Ihre Namen: Gruppe: Evolutionsbiologie 2, WS2015/2016: Bioinformatik - Übung 1 Erstellen Sie bitte vor Beginn der Übung einen Ordner auf dem Desktop, in dem Sie alle benötigten Dateien speichern können
Ihre Namen: Gruppe: Evolutionsbiologie 2, WS2015/2016: Bioinformatik - Übung 1 Erstellen Sie bitte vor Beginn der Übung einen Ordner auf dem Desktop, in dem Sie alle benötigten Dateien speichern können
Algorithmische Bioinformatik
 lgorithmische Bioinformatik Stringalignment Ulf Leser Wissensmanagement in der Bioinformatik Inhalt dieser Vorlesung pproximative Stringvergleiche Dotplots Edit-bstand und lignment Naiver lgorithmus Ulf
lgorithmische Bioinformatik Stringalignment Ulf Leser Wissensmanagement in der Bioinformatik Inhalt dieser Vorlesung pproximative Stringvergleiche Dotplots Edit-bstand und lignment Naiver lgorithmus Ulf
RNA Sekundärstruktur
 R Sekundärstruktur Dipl. Math. Isabelle Schneider niversität öttingen Institut für Mikrobiologie und enetik bteilung für Bioinformatik 12.12.2005 (niversität öttingen) 1 / 40 Themen der Vorlesung 1 R Motivation
R Sekundärstruktur Dipl. Math. Isabelle Schneider niversität öttingen Institut für Mikrobiologie und enetik bteilung für Bioinformatik 12.12.2005 (niversität öttingen) 1 / 40 Themen der Vorlesung 1 R Motivation
BI BIL E GK?? 1 BI GK HT 2 Seite 1 von 5. Abiturprüfung Biologie, Grundkurs
 Seite 1 von 5 biturprüfung 2009 Biologie, rundkurs ufgabenstellung: Thema: endiagnostik am Beispiel von Faktor-V-Leiden II.1 Erläutern Sie anhand von Material und Material D, welche Mutation auf dem codogenen
Seite 1 von 5 biturprüfung 2009 Biologie, rundkurs ufgabenstellung: Thema: endiagnostik am Beispiel von Faktor-V-Leiden II.1 Erläutern Sie anhand von Material und Material D, welche Mutation auf dem codogenen
MOL.504 Analyse von DNA- und Proteinsequenzen. Datenbanken & Informationssysteme
 MOL.504 Analyse von DNA- und Proteinsequenzen Datenbanken & Informationssysteme Inhaltsübersicht Informationsysteme National Center for Biotechnology Information (NCBI) The European Bioinformatics Institute
MOL.504 Analyse von DNA- und Proteinsequenzen Datenbanken & Informationssysteme Inhaltsübersicht Informationsysteme National Center for Biotechnology Information (NCBI) The European Bioinformatics Institute
Evolution & Genetik (Beispiel Hämoglobin) Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de
 Evolution & Genetik (Beispiel Hämoglobin) Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de DNA (Desoxyribonukleinsäure) 5 3 CGATGTACATCG GCTACATGTAGC 3 5 Doppelhelix Basen: Adenin,
Evolution & Genetik (Beispiel Hämoglobin) Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de DNA (Desoxyribonukleinsäure) 5 3 CGATGTACATCG GCTACATGTAGC 3 5 Doppelhelix Basen: Adenin,
Aminosäuren. Seitenkette. -Kohlenstoffatom. Karboxilgruppe. Aminogruppe
 Proteine Aminosäuren 16 Seitenkette -Kohlenstoffatom Aminogruppe Karboxilgruppe Die Gruppen der Aminosäuren 17 Bildung der Peptidbindung Die strukturellen Ebenen der Proteine 18 Primär Struktur Aminosäuer
Proteine Aminosäuren 16 Seitenkette -Kohlenstoffatom Aminogruppe Karboxilgruppe Die Gruppen der Aminosäuren 17 Bildung der Peptidbindung Die strukturellen Ebenen der Proteine 18 Primär Struktur Aminosäuer
Eine RNA-Menagerie: mirnas und andere kodierende und nichtkodierende RNAs
 Eine RN-Menagerie: mirns und andere kodierende und nichtkodierende RNs Peter N. Robinson Institut für medizinische Genetik harité Universitätsmedizin Berlin 23. Juni 2008 Peter N. Robinson (harité) RN
Eine RN-Menagerie: mirns und andere kodierende und nichtkodierende RNs Peter N. Robinson Institut für medizinische Genetik harité Universitätsmedizin Berlin 23. Juni 2008 Peter N. Robinson (harité) RN
Genannotation bei Prokaryoten
 Genannotation bei Prokaryoten Maike Tech Abt. Bioinformatik Institut für Mikrobiologie und Genetik (IMG) Universität Göttingen 28. November 2005 Genetik von Pro- und Eukaryoten Eukaryoten Prokaryoten Zellkern
Genannotation bei Prokaryoten Maike Tech Abt. Bioinformatik Institut für Mikrobiologie und Genetik (IMG) Universität Göttingen 28. November 2005 Genetik von Pro- und Eukaryoten Eukaryoten Prokaryoten Zellkern
Studiengang Informatik der FH Gießen-Friedberg. Sequenz-Alignment. Jan Schäfer. WS 2006/07 Betreuer: Prof. Dr. Klaus Quibeldey-Cirkel
 Studiengang Informatik der FH Gießen-Friedberg Sequenz-Alignment Jan Schäfer WS 2006/07 Betreuer: Prof. Dr. Klaus Quibeldey-Cirkel Überblick Einführung Grundlagen Wann ist das Merkmal der Ähnlichkeit erfüllt?
Studiengang Informatik der FH Gießen-Friedberg Sequenz-Alignment Jan Schäfer WS 2006/07 Betreuer: Prof. Dr. Klaus Quibeldey-Cirkel Überblick Einführung Grundlagen Wann ist das Merkmal der Ähnlichkeit erfüllt?
Biologie + Informatik = Bioinformatik??? Dr. Ursula Rost Bioinformatics and Computational Biochemistry European Media Laboratory Heidelberg
 Biologie + Informatik = Bioinformatik??? Dr. Ursula Rost Bioinformatics and Computational Biochemistry European Media Laboratory Heidelberg Zur Person Ursula Rost Studium Diplom-Informatik, TU Clausthal
Biologie + Informatik = Bioinformatik??? Dr. Ursula Rost Bioinformatics and Computational Biochemistry European Media Laboratory Heidelberg Zur Person Ursula Rost Studium Diplom-Informatik, TU Clausthal
Algorithmische Bioinformatik
 lgorithmische Bioinformatik pproximatives Stringmatching Edit-bstand Ulf Leser Wissensmanagement in der Bioinformatik Ziele dieser Vorlesung Einstieg in exaktes approximatives Stringmatching Bedeutung
lgorithmische Bioinformatik pproximatives Stringmatching Edit-bstand Ulf Leser Wissensmanagement in der Bioinformatik Ziele dieser Vorlesung Einstieg in exaktes approximatives Stringmatching Bedeutung
Threading - Algorithmen
 Threading - Algorithmen Florian Lindemann 22.11.2007 Florian Lindemann () Threading - Algorithmen 22.11.2007 1 / 25 Gliederung 1 Prospect Scoring Function Algorithmus Weitere Eigenschaften Komplexität
Threading - Algorithmen Florian Lindemann 22.11.2007 Florian Lindemann () Threading - Algorithmen 22.11.2007 1 / 25 Gliederung 1 Prospect Scoring Function Algorithmus Weitere Eigenschaften Komplexität
Informationstechnologie in der Pflanzenzüchtung. Biocomputing in einem Züchtungsunternehmen. Andreas Menze KWS SAAT AG, Einbeck
 Informationstechnologie in der Pflanzenzüchtung Biocomputing in einem Züchtungsunternehmen Andreas Menze KWS SAAT AG, Einbeck Biocomputing in einem Züchtungsunternehmen Biocomputing Was ist das? Wozu wird
Informationstechnologie in der Pflanzenzüchtung Biocomputing in einem Züchtungsunternehmen Andreas Menze KWS SAAT AG, Einbeck Biocomputing in einem Züchtungsunternehmen Biocomputing Was ist das? Wozu wird
Vorlesung Evolutionäre Algorithmen
 Vorlesung Evolutionäre Algorithmen Dr. Nicole Drechsler, AG Rechnerarchitektur Raum 3480, Tel. 7391, nd@tzi.de Vorschlag für Prüfungskriterien: Bearbeitung einer praktischen (Programmier-) Aufgabe Fachgespräch
Vorlesung Evolutionäre Algorithmen Dr. Nicole Drechsler, AG Rechnerarchitektur Raum 3480, Tel. 7391, nd@tzi.de Vorschlag für Prüfungskriterien: Bearbeitung einer praktischen (Programmier-) Aufgabe Fachgespräch
Statistische Verfahren:
 Statistische Verfahren: Hidden-Markov-Modelle für Multiples Alignment Stochastic Context-Free Grammars (SCFGs) für RNA-Multiples Alignment Übersicht 1 1. Hidden-Markov-Models (HMM) für Multiples Alignment
Statistische Verfahren: Hidden-Markov-Modelle für Multiples Alignment Stochastic Context-Free Grammars (SCFGs) für RNA-Multiples Alignment Übersicht 1 1. Hidden-Markov-Models (HMM) für Multiples Alignment
Expression der genetischen Information Skript: Kapitel 5
 Prof. A. Sartori Medizin 1. Studienjahr Bachelor Molekulare Zellbiologie FS 2013 12. März 2013 Expression der genetischen Information Skript: Kapitel 5 5.1 Struktur der RNA 5.2 RNA-Synthese (Transkription)
Prof. A. Sartori Medizin 1. Studienjahr Bachelor Molekulare Zellbiologie FS 2013 12. März 2013 Expression der genetischen Information Skript: Kapitel 5 5.1 Struktur der RNA 5.2 RNA-Synthese (Transkription)
ASSEMBLY ALGORITHMS FOR NEXT-GENERATION SEQUENCING DATA
 ASSEMBLY ALGORITHMS FOR NEXT-GENERATION SEQUENCING DATA Jason R. Miller*, Sergey Koren, Granger Sutton Ein Vortrag von Sergej Tschernyschkow Friedrich-Schiller-Universität Jena 03. Mai 2010 SERGEJ TSCHERNYSCHKOW
ASSEMBLY ALGORITHMS FOR NEXT-GENERATION SEQUENCING DATA Jason R. Miller*, Sergey Koren, Granger Sutton Ein Vortrag von Sergej Tschernyschkow Friedrich-Schiller-Universität Jena 03. Mai 2010 SERGEJ TSCHERNYSCHKOW
Kapitel 7: Sequenzen- Alignierung in der Bioinformatik
 Kapitel 7: Sequenzen- Alignierung in der Bioinformatik VO Algorithm Engineering Professor Dr. Petra Mutzel Lehrstuhl für Algorithm Engineering, LS11 19. VO 14. Juni 2007 1 Literatur für diese VO Volker
Kapitel 7: Sequenzen- Alignierung in der Bioinformatik VO Algorithm Engineering Professor Dr. Petra Mutzel Lehrstuhl für Algorithm Engineering, LS11 19. VO 14. Juni 2007 1 Literatur für diese VO Volker
Nach Terpenen und Kohlenhydraten nun eine weitere große Klasse an Naturstoffen
 260 17. Aminosäuren, Peptide ach Terpenen und Kohlenhydraten nun eine weitere große Klasse an aturstoffen 17.1 Übersicht Analog zu ydroxycarbonsäuren α-, β-, γ- Aminocarbonsäuren möglich: 2 3 2 2 α-amino-essigsäure
260 17. Aminosäuren, Peptide ach Terpenen und Kohlenhydraten nun eine weitere große Klasse an aturstoffen 17.1 Übersicht Analog zu ydroxycarbonsäuren α-, β-, γ- Aminocarbonsäuren möglich: 2 3 2 2 α-amino-essigsäure
MOL.504 Analyse von DNA- und Proteinsequenzen. Modul 2 BLAST-Sequenzsuche und Sequenzvergleiche
 MOL.504 Analyse von DNA- und Proteinsequenzen Modul 2 BLAST-Sequenzsuche und Sequenzvergleiche Summary Modul 1 - Datenbanken Wo finde ich die DNA Sequenz meines Zielgens? Wie erhalte ich Info aus der DNA-Datenbank
MOL.504 Analyse von DNA- und Proteinsequenzen Modul 2 BLAST-Sequenzsuche und Sequenzvergleiche Summary Modul 1 - Datenbanken Wo finde ich die DNA Sequenz meines Zielgens? Wie erhalte ich Info aus der DNA-Datenbank
Homologie und Sequenzähnlichkeit. Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de
 Homologie und Sequenzähnlichkeit Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de Homologie Verwandtschaft aufgrund gleicher Abstammung basiert auf Speziation (Artbildung): aus einer
Homologie und Sequenzähnlichkeit Prof. Dr. Antje Krause FH Bingen 06721 / 409 253 akrause@fh-bingen.de Homologie Verwandtschaft aufgrund gleicher Abstammung basiert auf Speziation (Artbildung): aus einer
From gene to 3D model
 From gene to 3D model Ein neues Gen, was nun? 1. Database search 2. Mitglied einer Proteinfamilie spezifische Domänen 3. Gibt es Hinweise auf die Funktion, Lokalisierung 4. Expression des Gens 5. Modeling
From gene to 3D model Ein neues Gen, was nun? 1. Database search 2. Mitglied einer Proteinfamilie spezifische Domänen 3. Gibt es Hinweise auf die Funktion, Lokalisierung 4. Expression des Gens 5. Modeling
Einführung in die Biochemie Antworten zu den Übungsaufgaben
 Einführung in die Biochemie Antworten zu den Übungsaufgaben Dank Die vorliegenden Antworten zu den Übungsaufgaben für das Seminar zum Modul Einführung in die Biochemie wurden im Wintersemester 2014/2015
Einführung in die Biochemie Antworten zu den Übungsaufgaben Dank Die vorliegenden Antworten zu den Übungsaufgaben für das Seminar zum Modul Einführung in die Biochemie wurden im Wintersemester 2014/2015
Vorlesung Bioinformatik Protein Threading
 Vorlesung Bioinformatik Protein Threading Dr. Axel Mosig 18. Mai 2004 Vorhersage der Tertiärstruktur von Proteinen Ab Initio-Methoden (z.b. via Molecular Dynamics) sind rechenintensiv; nur in Einzelfällen
Vorlesung Bioinformatik Protein Threading Dr. Axel Mosig 18. Mai 2004 Vorhersage der Tertiärstruktur von Proteinen Ab Initio-Methoden (z.b. via Molecular Dynamics) sind rechenintensiv; nur in Einzelfällen
Bioinformatik. Methoden zur Vorhersage vo n RNA- und Proteinstrukture n. Gerhard Steger
 Bioinformatik Methoden zur Vorhersage vo n RNA- und Proteinstrukture n Gerhard Steger Vorwort ix Strukturvorhersage von Nukleinsäuren 1 Struktur und Funktion von RNA 3 1.1 RNA-Struktur fl 1.2 Thermodynamik
Bioinformatik Methoden zur Vorhersage vo n RNA- und Proteinstrukture n Gerhard Steger Vorwort ix Strukturvorhersage von Nukleinsäuren 1 Struktur und Funktion von RNA 3 1.1 RNA-Struktur fl 1.2 Thermodynamik
Sequenz Alignment Teil 2
 Sequenz Alignment Teil 2 14.11.03 Vorlesung Bioinformatik 1 Molekulare Biotechnologie Dr. Rainer König Besonderen Dank an Mark van der Linden, Mechthilde Falkenhahn und der Husar Biocomputing Service Gruppe
Sequenz Alignment Teil 2 14.11.03 Vorlesung Bioinformatik 1 Molekulare Biotechnologie Dr. Rainer König Besonderen Dank an Mark van der Linden, Mechthilde Falkenhahn und der Husar Biocomputing Service Gruppe
Einführung in die Bioinformatik
 Einführung in die Bioinformatik Kay Nieselt Integrative Transkriptomik Zentrum für Bioinformatik Tübingen Kay.Nieselt@uni-tuebingen.de SS 2012 5. Biologische Netzwerke - Gut vernetzt hält besser Überblick
Einführung in die Bioinformatik Kay Nieselt Integrative Transkriptomik Zentrum für Bioinformatik Tübingen Kay.Nieselt@uni-tuebingen.de SS 2012 5. Biologische Netzwerke - Gut vernetzt hält besser Überblick
RNA Strukturvorhersage
 RNA Strukturvorhersage Christian Pölitz Hauptseminar AFS Institut für Theoretische Informatik Fakultät für Informatik und Automatisierung Technische Universität Ilmenau 17. Juli 2007 Christian Pölitz (TU
RNA Strukturvorhersage Christian Pölitz Hauptseminar AFS Institut für Theoretische Informatik Fakultät für Informatik und Automatisierung Technische Universität Ilmenau 17. Juli 2007 Christian Pölitz (TU
VL Algorithmische BioInformatik (19710) WS2013/2014 Woche 16 - Mittwoch. Annkatrin Bressin Freie Universität Berlin
 VL Algorithmische BioInformatik (19710) WS2013/2014 Woche 16 - Mittwoch Annkatrin Bressin Freie Universität Berlin Vorlesungsthemen Part 1: Background Basics (4) 1. The Nucleic Acid World 2. Protein Structure
VL Algorithmische BioInformatik (19710) WS2013/2014 Woche 16 - Mittwoch Annkatrin Bressin Freie Universität Berlin Vorlesungsthemen Part 1: Background Basics (4) 1. The Nucleic Acid World 2. Protein Structure
Bioinformatik. Lokale Alignierung Gapkosten. Silke Trißl / Ulf Leser Wissensmanagement in der. Bioinformatik
 Bioinformatik Lokale Alignierung Gapkosten Silke Trißl / Ulf Leser Wissensmanagement in der Bioinformatik Inhalt dieser Vorlesung Ähnlichkeit Lokales und globales Alignment Gapped Alignment Silke Trißl:
Bioinformatik Lokale Alignierung Gapkosten Silke Trißl / Ulf Leser Wissensmanagement in der Bioinformatik Inhalt dieser Vorlesung Ähnlichkeit Lokales und globales Alignment Gapped Alignment Silke Trißl:
Datenspeicherung und Datenfluß in der Zelle - Grundlagen der Biochemie
 Datenspeicherung und Datenfluß in der Zelle - Grundlagen der Biochemie Datenspeicherung und Datenfluß der Zelle Transkription DNA RNA Translation Protein Aufbau I. Grundlagen der organischen Chemie und
Datenspeicherung und Datenfluß in der Zelle - Grundlagen der Biochemie Datenspeicherung und Datenfluß der Zelle Transkription DNA RNA Translation Protein Aufbau I. Grundlagen der organischen Chemie und
Einführung in die Bioinformatik Algorithmen zur Sequenzanalyse
 Einführung in die Bioinformatik Algorithmen zur Sequenzanalyse!! Vorläufige Fassung, nur einzelne Abschnitte!!!! Enthält wahrscheinlich noch viele Fehler!!!! Wird regelmäßig erweitert und verbessert!!
Einführung in die Bioinformatik Algorithmen zur Sequenzanalyse!! Vorläufige Fassung, nur einzelne Abschnitte!!!! Enthält wahrscheinlich noch viele Fehler!!!! Wird regelmäßig erweitert und verbessert!!
Vorlesung Biophysik I - Molekulare Biophysik Kalbitzer/Kremer/Ziegler
 Vorlesung Biophysik I - Molekulare Biophysik Kalbitzer/Kremer/Ziegler 23.10. Zelle 30.10. Biologische Makromoleküle I 06.11. Biologische Makromoleküle II 13.11. Nukleinsäuren-Origami (DNA, RNA) 20.11.
Vorlesung Biophysik I - Molekulare Biophysik Kalbitzer/Kremer/Ziegler 23.10. Zelle 30.10. Biologische Makromoleküle I 06.11. Biologische Makromoleküle II 13.11. Nukleinsäuren-Origami (DNA, RNA) 20.11.
Python im Bioinformatiker-Alltag
 Python im Bioinformatiker-Alltag Marcel Martin Bioinformatik für Hochdurchsatztechnologien, TU Dortmund 6. Oktober 2011 1 von 27 Worum gehts? Bioinformatik Löst Probleme in Biologie oder Medizin Teilbereich
Python im Bioinformatiker-Alltag Marcel Martin Bioinformatik für Hochdurchsatztechnologien, TU Dortmund 6. Oktober 2011 1 von 27 Worum gehts? Bioinformatik Löst Probleme in Biologie oder Medizin Teilbereich
Einführung in die Bioinformatik
 Einführung in die Bioinformatik SS 2012 1. Was ist Bioinformatik? Kay Nieselt Integrative Transkriptomik Zentrum für Bioinformatik Tübingen Kay.Nieselt@uni-tuebingen.de Ablauf und Formales Ringvorlesung
Einführung in die Bioinformatik SS 2012 1. Was ist Bioinformatik? Kay Nieselt Integrative Transkriptomik Zentrum für Bioinformatik Tübingen Kay.Nieselt@uni-tuebingen.de Ablauf und Formales Ringvorlesung
Aminosäuren - Proteine
 Aminosäuren - Proteine ÜBERBLICK D.Pflumm KSR / MSE Aminosäuren Überblick Allgemeine Formel für das Grundgerüst einer Aminosäure Carboxylgruppe: R-COOH O Aminogruppe: R-NH 2 einzelnes C-Atom (α-c-atom)
Aminosäuren - Proteine ÜBERBLICK D.Pflumm KSR / MSE Aminosäuren Überblick Allgemeine Formel für das Grundgerüst einer Aminosäure Carboxylgruppe: R-COOH O Aminogruppe: R-NH 2 einzelnes C-Atom (α-c-atom)
Vorlesung Einführung in die Bioinformatik
 Vorlesung Einführung in die Bioinformatik Dr. Stephan Weise 04.04.2016 Einführung Gegeben: zwei Sequenzen Gesucht: Ähnlichkeit quantitativ erfassen Entsprechungen zwischen einzelnen Bausteinen beider Sequenzen
Vorlesung Einführung in die Bioinformatik Dr. Stephan Weise 04.04.2016 Einführung Gegeben: zwei Sequenzen Gesucht: Ähnlichkeit quantitativ erfassen Entsprechungen zwischen einzelnen Bausteinen beider Sequenzen
Abiturprüfung Biologie, Grundkurs
 Seite 1 von 6 biturprüfung 2008 Biologie, rundkurs ufgabenstellung: Thema: Ein Krankheitsbild unterschiedliche rsachen II.1 Werten Sie die Materialien und B hinsichtlich der Risikofaktoren für Diabetes
Seite 1 von 6 biturprüfung 2008 Biologie, rundkurs ufgabenstellung: Thema: Ein Krankheitsbild unterschiedliche rsachen II.1 Werten Sie die Materialien und B hinsichtlich der Risikofaktoren für Diabetes
Aufbau, Struktur, Funktion von DNA, RNA und Proteinen
 Aufbau, Struktur, Funktion von DNA, RNA und Proteinen Mitarbeiterseminar der Medizinischen Fakultät Ruhr-Universität Bochum Andreas Friebe Abteilung für Pharmakologie und Toxikologie Aufbau, Struktur,
Aufbau, Struktur, Funktion von DNA, RNA und Proteinen Mitarbeiterseminar der Medizinischen Fakultät Ruhr-Universität Bochum Andreas Friebe Abteilung für Pharmakologie und Toxikologie Aufbau, Struktur,
Algorithmische Bioinformatik
 Algorithmische Bioinformatik Effiziente Berechnung des Editabstands Dynamische Programmierung Ulf Leser Wissensmanagement in der Bioinformatik Inhalt dieser Vorlesung Rekursive Definition des Editabstands
Algorithmische Bioinformatik Effiziente Berechnung des Editabstands Dynamische Programmierung Ulf Leser Wissensmanagement in der Bioinformatik Inhalt dieser Vorlesung Rekursive Definition des Editabstands
Bioinformatik I. Zentrum für Bioinformatik der Universität des Saarlandes WS 2001/2002
 Bioinformatik I Zentrum für Bioinformatik der Universität des Saarlandes WS 2001/2002 Der Bauplan des Menschen Das menschliche Genom G ATGC TACG T C A Die Chromosomen Die (46) Chromosomen sind die Träger
Bioinformatik I Zentrum für Bioinformatik der Universität des Saarlandes WS 2001/2002 Der Bauplan des Menschen Das menschliche Genom G ATGC TACG T C A Die Chromosomen Die (46) Chromosomen sind die Träger
Statistische Methoden in der Bioinformatik
 Statistische Methoden in der Bioinformatik Prof. Dr. Jörg Rahnenführer Raum 720 Email: rahnenfuehrer@statistik. tu-.de Voraussetzungen: Vordiplom in Statistik, Mathematik, Datenanalyse, Informatik Zeiten
Statistische Methoden in der Bioinformatik Prof. Dr. Jörg Rahnenführer Raum 720 Email: rahnenfuehrer@statistik. tu-.de Voraussetzungen: Vordiplom in Statistik, Mathematik, Datenanalyse, Informatik Zeiten
8. Translation. Konzepte: Translation benötigt trnas und Ribosomen. Genetischer Code. Initiation - Elongation - Termination
 8. Translation Konzepte: Translation benötigt trnas und Ribosomen Genetischer Code Initiation - Elongation - Termination 1. Welche Typen von RNAs gibt es und welches sind ihre Funktionen? mouse human bacteria
8. Translation Konzepte: Translation benötigt trnas und Ribosomen Genetischer Code Initiation - Elongation - Termination 1. Welche Typen von RNAs gibt es und welches sind ihre Funktionen? mouse human bacteria
Wichtige Themen aus der Vorlesung Bioinformatik I WS 2013/2014
 Universität des Saarlandes FR 6.2 Informatik Prof. Dr. Hans-Peter Lenhof Daniel Stöckel, M. Sc. Patrick Trampert, M. Sc. Lara Schneider, M. Sc. I Wichtige Themen aus der Vorlesung Bioinformatik I WS 2013/2014
Universität des Saarlandes FR 6.2 Informatik Prof. Dr. Hans-Peter Lenhof Daniel Stöckel, M. Sc. Patrick Trampert, M. Sc. Lara Schneider, M. Sc. I Wichtige Themen aus der Vorlesung Bioinformatik I WS 2013/2014
Algorithmen auf Sequenzen 12.04.2010
 Algorithmen auf Sequenzen 12.04.2010 Prof. Dr. Sven Rahmann 1 Team Prof. Dr. Sven Rahmann Dipl.-Inform Tobias Marschall (Skript) Zeit Mo 8:30-10; Übungen Mi 8:30-10 ca. alle 2 Wochen (Plan!) Ort OH14,
Algorithmen auf Sequenzen 12.04.2010 Prof. Dr. Sven Rahmann 1 Team Prof. Dr. Sven Rahmann Dipl.-Inform Tobias Marschall (Skript) Zeit Mo 8:30-10; Übungen Mi 8:30-10 ca. alle 2 Wochen (Plan!) Ort OH14,
Typische Speicherfehler in C
 Typische Speicherfehler in C Thorsten Ploß Informatik Universität Hamburg Proseminar: C-Grundlagen und Konzepte 17.05.2013 1 / 13 Inhaltsverzeichnis Einleitung Klassische Speicherverwaltung - Fehlerquellen
Typische Speicherfehler in C Thorsten Ploß Informatik Universität Hamburg Proseminar: C-Grundlagen und Konzepte 17.05.2013 1 / 13 Inhaltsverzeichnis Einleitung Klassische Speicherverwaltung - Fehlerquellen
Gliederung. Algorithmen und Datenstrukturen II. Problem: Längste gemeinsame Teilsequenz. Problem: Längste gemeinsame Teilsequenz
 Gliederung Algorithmen und Datenstrukturen II Algorithmen zur Textverarbeitung II D. Rösner Institut für Wissens- und Sprachverarbeitung Fakultät für Informatik Otto-von-Guericke Universität Magdeburg
Gliederung Algorithmen und Datenstrukturen II Algorithmen zur Textverarbeitung II D. Rösner Institut für Wissens- und Sprachverarbeitung Fakultät für Informatik Otto-von-Guericke Universität Magdeburg
Bioinformatik I (Einführung)
 Kay Diederichs, Sommersemester 2015 Bioinformatik I (Einführung) Algorithmen Sequenzen Strukturen PDFs unter http://strucbio.biologie.unikonstanz.de/~dikay/bioinformatik/ Klausur: Fr 17.7. 10:00-11:00
Kay Diederichs, Sommersemester 2015 Bioinformatik I (Einführung) Algorithmen Sequenzen Strukturen PDFs unter http://strucbio.biologie.unikonstanz.de/~dikay/bioinformatik/ Klausur: Fr 17.7. 10:00-11:00
Bioinformatik. Substitutionsmatrizen BLAST. Ulf Leser Wissensmanagement in der. Bioinformatik
 Bioinformatik Substitutionsmatrizen BLAST Ulf Leser Wissensmanagement in der Bioinformatik Inhalt dieser Vorlesung Substitutionsmatrizen: PAM und BLOSSUM Suche in Datenbanken: Basic Local Alignment Search
Bioinformatik Substitutionsmatrizen BLAST Ulf Leser Wissensmanagement in der Bioinformatik Inhalt dieser Vorlesung Substitutionsmatrizen: PAM und BLOSSUM Suche in Datenbanken: Basic Local Alignment Search
DNS-Modell Best.-Nr. 2015801
 DNS-Modell Best.-Nr. 2015801 1. Produktvorstellung Ziel des Produktes Dieses Modell soll das DNS-Molekül visualisieren: es soll die Doppelspirale, Stickstoffbasen mit Wasserstoffbrückenbindung, Zucker-Phosphatskelette
DNS-Modell Best.-Nr. 2015801 1. Produktvorstellung Ziel des Produktes Dieses Modell soll das DNS-Molekül visualisieren: es soll die Doppelspirale, Stickstoffbasen mit Wasserstoffbrückenbindung, Zucker-Phosphatskelette
Einführung in die Programmierung
 : Inhalt Einführung in die Programmierung Wintersemester 2009/0 : Technik vs. Iteration Prof. Dr. Günter Rudolph Lehrstuhl für Algorithm Engineering Fakultät für Informatik TU Dortmund 2 Definition (einfache,
: Inhalt Einführung in die Programmierung Wintersemester 2009/0 : Technik vs. Iteration Prof. Dr. Günter Rudolph Lehrstuhl für Algorithm Engineering Fakultät für Informatik TU Dortmund 2 Definition (einfache,
Bioinformatik: Schnittstelle zwischen Informatik und Life-Science
 Bioinformatik: Schnittstelle zwischen Informatik und Life-Science Andreas Zendler (PD Dr.rer.nat.Dr.phil.) GI / GChACM 12. ovember 2001 Inhaltsübersicht I. Einführung II. Bioinformatik III. Industrial
Bioinformatik: Schnittstelle zwischen Informatik und Life-Science Andreas Zendler (PD Dr.rer.nat.Dr.phil.) GI / GChACM 12. ovember 2001 Inhaltsübersicht I. Einführung II. Bioinformatik III. Industrial
Bei Einbeziehung von neun Allelen in den Vergleich ergibt sich eine Mutation in 38 Generationen (350:9); das entspricht ca. 770 Jahren.
 336 DNA Genealogie Das Muster genetischer Variationen im Erbgut einer Person - zu gleichen Teilen von Mutter und Vater ererbt - definiert seine genetische Identität unveränderlich. Neben seiner Identität
336 DNA Genealogie Das Muster genetischer Variationen im Erbgut einer Person - zu gleichen Teilen von Mutter und Vater ererbt - definiert seine genetische Identität unveränderlich. Neben seiner Identität
Algorithms and Hardness Results for DNA Physical Mapping, Protein Identification, and Related Combinatorial Problems
 Diss. ETH No. 15258, 2003 Algorithms and Hardness Results for DNA Physical Mapping, Protein Identification, and Related Combinatorial Problems A dissertation submitted to the Swiss Federal Institute of
Diss. ETH No. 15258, 2003 Algorithms and Hardness Results for DNA Physical Mapping, Protein Identification, and Related Combinatorial Problems A dissertation submitted to the Swiss Federal Institute of
RNA- und DNA-Strukturen Strukturelle Bioinformatik WS15/16
 RNA- und DNA-Strukturen Strukturelle Bioinformatik WS15/16 Dr. Stefan Simm, 02.12.2015 simm@bio.uni-frankfurt.de RNA- und DNA-Strukturen DNA Historie der DNA Friedrich Miescher (1869) entdeckte in einem
RNA- und DNA-Strukturen Strukturelle Bioinformatik WS15/16 Dr. Stefan Simm, 02.12.2015 simm@bio.uni-frankfurt.de RNA- und DNA-Strukturen DNA Historie der DNA Friedrich Miescher (1869) entdeckte in einem
Resistenz gegen HIV (Computer- und Internet-basierte Aufgabe)
 1 Resistenz gegen HIV (Computer- und Internet-basierte Aufgabe) In den frühen 1990er Jahren zeigten verschiedene Untersuchungen, dass einige Menschen trotz wiederholten Kontaktes mit dem HI-Virus nicht
1 Resistenz gegen HIV (Computer- und Internet-basierte Aufgabe) In den frühen 1990er Jahren zeigten verschiedene Untersuchungen, dass einige Menschen trotz wiederholten Kontaktes mit dem HI-Virus nicht
Sequenzen-Alignierung in der Bioinformatik
 Sequenzen-Alignierung in der Bioinformatik VO Algorithm Engineering Professor Dr. Petra Mutzel Lehrstuhl für Algorithm Engineering, LS 22. VO 23..26 Literatur für diese VO Volker Heun: Skriptum zur Vorlesung
Sequenzen-Alignierung in der Bioinformatik VO Algorithm Engineering Professor Dr. Petra Mutzel Lehrstuhl für Algorithm Engineering, LS 22. VO 23..26 Literatur für diese VO Volker Heun: Skriptum zur Vorlesung
Aminosäurenanalytik. Probenvorbereitung Eiweißfällung, Oxidation und Hydrolyse Karl-Heinz Jansen SYKAM CHROMATOGRAPHIE
 Aminosäurenanalytik Probenvorbereitung Eiweißfällung, Oxidation und Hydrolyse Karl-Heinz Jansen SYKAM CHROMATOGRAPHIE Proteinfällung 2 Proteinfällung 3 Proteinfällung 4 Proteinfällung 5 Proteinfällung
Aminosäurenanalytik Probenvorbereitung Eiweißfällung, Oxidation und Hydrolyse Karl-Heinz Jansen SYKAM CHROMATOGRAPHIE Proteinfällung 2 Proteinfällung 3 Proteinfällung 4 Proteinfällung 5 Proteinfällung
Molekularbiologische Datenbanken
 Molekularbiologische Datenbanken Übungen Sommersemester 2004 Silke Trißl Prof. Ulf Leser Wissensmanagement in der Bioinformatik Organisatorisches Mittwoch 11 13 Uhr, RUD26 0'313 Mi, 05. Mai 2004 entfällt
Molekularbiologische Datenbanken Übungen Sommersemester 2004 Silke Trißl Prof. Ulf Leser Wissensmanagement in der Bioinformatik Organisatorisches Mittwoch 11 13 Uhr, RUD26 0'313 Mi, 05. Mai 2004 entfällt
DATENQUALITÄT IN GENOMDATENBANKEN
 DATENQUALITÄT IN GENOMDATENBANKEN Alexander Fehr 28. Januar 2004 Gliederung Motivation Biologische Grundkonzepte Genomdaten Datenproduktion und Fehler Data Cleansing 2 Motivation (1) Genomdatenbanken enthalten
DATENQUALITÄT IN GENOMDATENBANKEN Alexander Fehr 28. Januar 2004 Gliederung Motivation Biologische Grundkonzepte Genomdaten Datenproduktion und Fehler Data Cleansing 2 Motivation (1) Genomdatenbanken enthalten
Übung II. Einführung, Teil 1. Arbeiten mit Ensembl
 Übung II Einführung, Teil 1 Arbeiten mit Ensembl Ensembl Genome Browser (Bereitstellung von Vielzeller Genomen) Projekt wurde 1999 initiiert Projektpartner EMBL European Bioinformatics Institute (EBI)
Übung II Einführung, Teil 1 Arbeiten mit Ensembl Ensembl Genome Browser (Bereitstellung von Vielzeller Genomen) Projekt wurde 1999 initiiert Projektpartner EMBL European Bioinformatics Institute (EBI)
Algorithmische Bioinformatik 1
 Algorithmische Bioinformatik 1 Dr. Hanjo Täubig Lehrstuhl für Effiziente Algorithmen (Prof. Dr. Ernst W. Mayr) Institut für Informatik Technische Universität München Sommersemester 2009 Übersicht Paarweises
Algorithmische Bioinformatik 1 Dr. Hanjo Täubig Lehrstuhl für Effiziente Algorithmen (Prof. Dr. Ernst W. Mayr) Institut für Informatik Technische Universität München Sommersemester 2009 Übersicht Paarweises
Construction of Protein Binding Sites in Scaffold Structures
 Construction of Protein Binding Sites in Scaffold Structures Shide Liang, Zhijie Liu, Weizhong Li, Lisheng Ni, Luhua Lai Peking University, Beijing Seminar Bioinformatik SS05 Präsentation: Mareike Moritz
Construction of Protein Binding Sites in Scaffold Structures Shide Liang, Zhijie Liu, Weizhong Li, Lisheng Ni, Luhua Lai Peking University, Beijing Seminar Bioinformatik SS05 Präsentation: Mareike Moritz
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2014
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2014 Fragen für die Übungsstunde 8 (14.07-18.07.) 1) Von der DNA-Sequenz zum Protein Sie können
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2014 Fragen für die Übungsstunde 8 (14.07-18.07.) 1) Von der DNA-Sequenz zum Protein Sie können
Die Suche nach Genen in Bakteriengenomen. BWInf-Workshop 22.-23. März 2011. Prof. Dr. Sven Rahmann AG Bioinformatik Informatik XI, TU Dortmund
 Die Suche nach Genen in Bakteriengenomen BWInf-Workshop 22.-23. März 2011 Prof. Dr. Sven Rahmann AG Bioinformatik Informatik XI, TU Dortmund 1 Bioinformatik was ist das? Aufgabe: Analyse (molekular)biologischer
Die Suche nach Genen in Bakteriengenomen BWInf-Workshop 22.-23. März 2011 Prof. Dr. Sven Rahmann AG Bioinformatik Informatik XI, TU Dortmund 1 Bioinformatik was ist das? Aufgabe: Analyse (molekular)biologischer
Vorlesung Einführung in die Bioinformatik
 Vorlesung Einführung in die Bioinformatik Organisatorische Hinweise Dr. Uwe Scholz 07.04.2014 Informationen Uwe Scholz: scholz@ipk-gatersleben.de Lothar Altschmied: lothar@ipk-gatersleben.de Christian
Vorlesung Einführung in die Bioinformatik Organisatorische Hinweise Dr. Uwe Scholz 07.04.2014 Informationen Uwe Scholz: scholz@ipk-gatersleben.de Lothar Altschmied: lothar@ipk-gatersleben.de Christian
Vorlesung Molekulare Humangenetik
 Vorlesung Molekulare Humangenetik WS 2013/2014 Dr. Shamsadin DNA-RNA-Protein Allgemeines Prüfungen o. Klausuren als indiv. Ergänzung 3LP benotet o. unbenotet Seminar Block 2LP Vorlesung Donnerstags 14-16
Vorlesung Molekulare Humangenetik WS 2013/2014 Dr. Shamsadin DNA-RNA-Protein Allgemeines Prüfungen o. Klausuren als indiv. Ergänzung 3LP benotet o. unbenotet Seminar Block 2LP Vorlesung Donnerstags 14-16
Molekularbiologische Grundlagen
 Molekularbiologische Grundlagen Ulf Leser, Sommersemester 2008 Silke Trißl Überblick Biologie Organismen Aufbau von Zellen Prokaryoten und Eukaryoten Genom und DNA Transkription DNA RNA Protein Proteine
Molekularbiologische Grundlagen Ulf Leser, Sommersemester 2008 Silke Trißl Überblick Biologie Organismen Aufbau von Zellen Prokaryoten und Eukaryoten Genom und DNA Transkription DNA RNA Protein Proteine
Eine neue RNA-Welt. Uralte RNA-Welt Am Anfang der Entstehung des Lebens. Bekannte RNA-Welt Protein-Synthese. Neue RNA-Welt Regulatorische RNA-Moleküle
 RNAs Eine neue RNA-Welt 1. Uralte RNA-Welt Am Anfang der Entstehung des Lebens Bekannte RNA-Welt Protein-Synthese Neue RNA-Welt Regulatorische RNA-Moleküle 2. Eine neue RNA-Welt die Anzahl der nicht-kodierenden
RNAs Eine neue RNA-Welt 1. Uralte RNA-Welt Am Anfang der Entstehung des Lebens Bekannte RNA-Welt Protein-Synthese Neue RNA-Welt Regulatorische RNA-Moleküle 2. Eine neue RNA-Welt die Anzahl der nicht-kodierenden
Gen Protein Aufgaben: Edel LK-Bio BI-3
 Proteinbiosynthese Von der DNA zum Protein Dieses Lernprogramm zeigt Ihnen in einem vereinfachten Modell den im Zellinneren ablaufenden Prozess vom Gen auf der DNA zum Protein. Aufgaben: 1 Betrachten Sie
Proteinbiosynthese Von der DNA zum Protein Dieses Lernprogramm zeigt Ihnen in einem vereinfachten Modell den im Zellinneren ablaufenden Prozess vom Gen auf der DNA zum Protein. Aufgaben: 1 Betrachten Sie
Die wichtigsten Bioinformatikdatenbanken. SwissProt, PDB, Scop, CATH, FSSP, PROSITE, Pfam
 Die wichtigsten Bioinformatikdatenbanken SwissProt, PDB, Scop, CATH, FSSP, PROSITE, Pfam Übersicht Nucleotidsequenzen: GenBank, EMBL Proteindatenbank SwissProt Proteinstrukturen: Brookhavens PDB Proteinklassifizierung:
Die wichtigsten Bioinformatikdatenbanken SwissProt, PDB, Scop, CATH, FSSP, PROSITE, Pfam Übersicht Nucleotidsequenzen: GenBank, EMBL Proteindatenbank SwissProt Proteinstrukturen: Brookhavens PDB Proteinklassifizierung:
Codierung und Repräsentation
 Codierung und Repräsentation - Biologie - Block 4 Codierung und Repräsentation Folie: 1 Codierung: Genotyp und Phänotypebene Vier Übergänge eines evolutionären Zyklus (nach Lewontin, 1974) T 1 : Die Verteilung
Codierung und Repräsentation - Biologie - Block 4 Codierung und Repräsentation Folie: 1 Codierung: Genotyp und Phänotypebene Vier Übergänge eines evolutionären Zyklus (nach Lewontin, 1974) T 1 : Die Verteilung
Genomsequenzierung für Anfänger
 Genomsequenzierung für Anfänger Philipp Pagel 8. November 2005 1 DNA Sequenzierung Heute wird DNA üblicherweise mit der sogenannten Sanger (oder chain-terminationoder Didesoxy-) Methode sequenziert dessen
Genomsequenzierung für Anfänger Philipp Pagel 8. November 2005 1 DNA Sequenzierung Heute wird DNA üblicherweise mit der sogenannten Sanger (oder chain-terminationoder Didesoxy-) Methode sequenziert dessen
5.2. Differenzierung und Quantifizierung von Rind und Schwein mittels Real-Time PCR
 5.2. Differenzierung und Quantifizierung von Rind und Schwein mittels Real-Time PR Im Laufe der Zeit wurde bei dieser rbeit die Differenzierung und Quantifizierung der DN von Schwein und Rind in den Vordergrund
5.2. Differenzierung und Quantifizierung von Rind und Schwein mittels Real-Time PR Im Laufe der Zeit wurde bei dieser rbeit die Differenzierung und Quantifizierung der DN von Schwein und Rind in den Vordergrund
FOR MUW SSM3 (2008) STUDENTS EDUCATIONAL PURPOSE ONLY
 Angewandte Bioinformatik Grundlagen der Annotation von eukaryotischen Genomen Online Datenbanken und Bioinformatik Tools Sequenzen Sequenzalignment: Fasta und Blast Motive und Hidden Markov Models Genom-Browser
Angewandte Bioinformatik Grundlagen der Annotation von eukaryotischen Genomen Online Datenbanken und Bioinformatik Tools Sequenzen Sequenzalignment: Fasta und Blast Motive und Hidden Markov Models Genom-Browser
Von der DNA zur Datenbank: Sequenzierung & Assemblierung
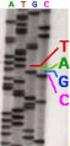 Vorlesung Einführung in die Bioinforma4k SoSe 2012 Von der DN zur Datenbank: Sequenzierung & ssemblierung Prof. Daniel Huson ZBI enter for Bioinformatics Entdeckung der DN Friedrich Miescher (1844-1895)
Vorlesung Einführung in die Bioinforma4k SoSe 2012 Von der DN zur Datenbank: Sequenzierung & ssemblierung Prof. Daniel Huson ZBI enter for Bioinformatics Entdeckung der DN Friedrich Miescher (1844-1895)
Bioinformatik an der FH Bingen
 Bioinformatik an der FH Bingen Prof. Dr. Antje Krause 05.11.2010 Wie alles begann... 1955 erste Proteinsequenz (nach 12 Jahren Arbeit) veröffentlicht (Insulin vom Rind) Frederick Sanger MALWTRLRPLLALLALWPPPPA
Bioinformatik an der FH Bingen Prof. Dr. Antje Krause 05.11.2010 Wie alles begann... 1955 erste Proteinsequenz (nach 12 Jahren Arbeit) veröffentlicht (Insulin vom Rind) Frederick Sanger MALWTRLRPLLALLALWPPPPA
Epigenetik. J. Breckow
 Felder der strahlenbiologischen Forschung : Klassische Strahlenbiologie : Dosis-Wirkungsbeziehungen für zelluläre Effekte (z.b. Überlebenskurven, Proliferationsfähigkeit, RBW, ) (Klassische) Molekulare
Felder der strahlenbiologischen Forschung : Klassische Strahlenbiologie : Dosis-Wirkungsbeziehungen für zelluläre Effekte (z.b. Überlebenskurven, Proliferationsfähigkeit, RBW, ) (Klassische) Molekulare
Fernstudium "Molekulare Evolution" Bernhard Lieb Michael Schaffeld. Institut für Zoologie Universität Mainz
 Fernstudium "Molekulare Evolution" ernhard Lieb Michael Schaffeld Institut für Zoologie Universität Mainz 1 Ziel des Kurses Wie erhalte ich aus meinen (Sequenz-) aten einen Stammbaum, und was sagt mir
Fernstudium "Molekulare Evolution" ernhard Lieb Michael Schaffeld Institut für Zoologie Universität Mainz 1 Ziel des Kurses Wie erhalte ich aus meinen (Sequenz-) aten einen Stammbaum, und was sagt mir
MOL.504 Analyse von DNA- und Proteinsequenzen. Übungsaufgaben BLAST-Sequenzsuche und -vergleiche
 MOL.504 Analyse von DNA- und Proteinsequenzen Übungsaufgaben BLAST-Sequenzsuche und -vergleiche Ü6a blastn und blastx Verwenden Sie die in Übung 3 (Datenbanken) gefundene yqjm-sequenz aus Bacillus subtilis
MOL.504 Analyse von DNA- und Proteinsequenzen Übungsaufgaben BLAST-Sequenzsuche und -vergleiche Ü6a blastn und blastx Verwenden Sie die in Übung 3 (Datenbanken) gefundene yqjm-sequenz aus Bacillus subtilis
4. Genetische Mechanismen bei Bakterien
 4. Genetische Mechanismen bei Bakterien 4.1 Makromoleküle und genetische Information Aufbau der DNA Phasen des Informationsflusses Vergleich der Informationsübertragung bei Pro- und Eukaryoten 4.2 Struktur
4. Genetische Mechanismen bei Bakterien 4.1 Makromoleküle und genetische Information Aufbau der DNA Phasen des Informationsflusses Vergleich der Informationsübertragung bei Pro- und Eukaryoten 4.2 Struktur
Modul 8: Bioinformatik A. Von der DNA zum Protein Proteinsynthese in silicio
 Modul 8: Bioinformatik A. Von der DNA zum Protein Proteinsynthese in silicio Ein Wissenschaftler erhält nach einer Sequenzierung folgenden Ausschnitt aus einer DNA-Sequenz: 5 ctaccatcaa tccggtaggt tttccggctg
Modul 8: Bioinformatik A. Von der DNA zum Protein Proteinsynthese in silicio Ein Wissenschaftler erhält nach einer Sequenzierung folgenden Ausschnitt aus einer DNA-Sequenz: 5 ctaccatcaa tccggtaggt tttccggctg
Wichtige Themen aus der Vorlesung Bioinformatik II SS 2014
 Universität des Saarlandes FR 6.2 Informatik Prof. Dr. Hans-Peter Lenhof M. Sc. Daniel Stöckel M. Sc. Patrick Trampert M. Sc. Lara Schneider Wichtige Themen aus der Vorlesung Bioinformatik II SS 2014 Hinweis:
Universität des Saarlandes FR 6.2 Informatik Prof. Dr. Hans-Peter Lenhof M. Sc. Daniel Stöckel M. Sc. Patrick Trampert M. Sc. Lara Schneider Wichtige Themen aus der Vorlesung Bioinformatik II SS 2014 Hinweis:
PCR basierte- Detektionstechniken
 PCR basierte- Detektionstechniken Warum überhaupt? Forensische Analysen: Vaterschaftstests, Kriminalistik Mikrobielle Gemeinschaften: Biofilme, medizinische Mikrobiologie 2 Warum überhaupt? minimale Mengen
PCR basierte- Detektionstechniken Warum überhaupt? Forensische Analysen: Vaterschaftstests, Kriminalistik Mikrobielle Gemeinschaften: Biofilme, medizinische Mikrobiologie 2 Warum überhaupt? minimale Mengen
Read Mapping Projektmanagement im So3warebereich SeqAn
 Read Mapping Projektmanagement im So3warebereich SeqAn David Weese April 2010 Inhalt Einführung Reads erzeugen read simulator SWP Teilprojekte Projektplan EINFÜHRUNG 2 nd /Next GeneraGon Sequencing Technologien:
Read Mapping Projektmanagement im So3warebereich SeqAn David Weese April 2010 Inhalt Einführung Reads erzeugen read simulator SWP Teilprojekte Projektplan EINFÜHRUNG 2 nd /Next GeneraGon Sequencing Technologien:
Kraftfeldmethoden von der Energieminimierung zur Moleküldynamik. Frank Cordes
 Kraftfeldmethoden von der Energieminimierung zur Moleküldynamik Frank Cordes Vorlesung Algorithmische Bioinformatik, WS 2004/05 12. Januar 2005 Konformationsgenerierung: Levinthal Paradoxon Ein Protein
Kraftfeldmethoden von der Energieminimierung zur Moleküldynamik Frank Cordes Vorlesung Algorithmische Bioinformatik, WS 2004/05 12. Januar 2005 Konformationsgenerierung: Levinthal Paradoxon Ein Protein
1. Die Gene befinden sich im Zellkern. Zellleib. 2. Chromosomen bestehen aus DNA. 4. Ein Gen ist ein DNA-Abschnitt 7. Protein-Herstellung nach Bedarf
 rundlagen 1. Die ene befinden sich im Zellkern 3. lle hromosomen zusammen bilden das enom Zellleib Bakterium Pflanzenzelle menschliches enom Zellkern Muskelzelle Nervenzelle DN 2. hromosomen bestehen aus
rundlagen 1. Die ene befinden sich im Zellkern 3. lle hromosomen zusammen bilden das enom Zellleib Bakterium Pflanzenzelle menschliches enom Zellkern Muskelzelle Nervenzelle DN 2. hromosomen bestehen aus
Programmiersprachen in der Bioinformatik
 Programmiersprachen in der Bioinformatik Bioinformatik In der Biologie immer größere Datenmengen (z.b. Genome, Proteinsequenzen) Sequenzanalyse, Strukturvorhersage Informationen in Datenbanken abrufbar
Programmiersprachen in der Bioinformatik Bioinformatik In der Biologie immer größere Datenmengen (z.b. Genome, Proteinsequenzen) Sequenzanalyse, Strukturvorhersage Informationen in Datenbanken abrufbar
Mathematik und Naturwissenschaften, Biologie, Biochemie. Biochemie II - Tutorium
 Mathematik und Naturwissenschaften, Biologie, Biochemie Biochemie II - Tutorium Dresden, 12.10.2016 Alexander Götze 3.Semester Molekulare Biotechnologie a.goetze2207@googlemail.com Mi. 2DS DRU. 68 H Michel
Mathematik und Naturwissenschaften, Biologie, Biochemie Biochemie II - Tutorium Dresden, 12.10.2016 Alexander Götze 3.Semester Molekulare Biotechnologie a.goetze2207@googlemail.com Mi. 2DS DRU. 68 H Michel
Das zentrale Dogma der Molekularbiologie:
 Das zentrale Dogma der Molekularbiologie: DNA Transkription RNA Translation Protein 1 Begriffserklärungen GENOM: Ist die allgemeine Bezeichnung für die Gesamtheit aller Gene eines Organismus GEN: Ist ein
Das zentrale Dogma der Molekularbiologie: DNA Transkription RNA Translation Protein 1 Begriffserklärungen GENOM: Ist die allgemeine Bezeichnung für die Gesamtheit aller Gene eines Organismus GEN: Ist ein
Neue DNA Sequenzierungstechnologien im Überblick
 Neue DNA Sequenzierungstechnologien im Überblick Dr. Bernd Timmermann Next Generation Sequencing Core Facility Max Planck Institute for Molecular Genetics Berlin, Germany Max-Planck-Gesellschaft 80 Institute
Neue DNA Sequenzierungstechnologien im Überblick Dr. Bernd Timmermann Next Generation Sequencing Core Facility Max Planck Institute for Molecular Genetics Berlin, Germany Max-Planck-Gesellschaft 80 Institute
Mathematik und Naturwissenschaften, Biologie, Biochemie. Biochemie II - Tutorium
 Mathematik und Naturwissenschaften, Biologie, Biochemie Biochemie II - Tutorium Dresden, 20.10.2016 Alexander Götze 3.Semester Molekulare Biotechnologie a.goetze2207@googlemail.com Mi. 2DS DRU. 68 H Michel
Mathematik und Naturwissenschaften, Biologie, Biochemie Biochemie II - Tutorium Dresden, 20.10.2016 Alexander Götze 3.Semester Molekulare Biotechnologie a.goetze2207@googlemail.com Mi. 2DS DRU. 68 H Michel
Sequenz- und Kommunikationsdiagrammen. Systemmodellierung mit SysML von Michel Manthey
 Sequenz- und Kommunikationsdiagrammen von Michel Manthey 1 Interaktionsdiagramme Sequenzdiagramme (auch in SysML) Kommunikationsdiagramme Zeitdiagramme Interaktionsübersichtsdiagramme von Michel Manthey
Sequenz- und Kommunikationsdiagrammen von Michel Manthey 1 Interaktionsdiagramme Sequenzdiagramme (auch in SysML) Kommunikationsdiagramme Zeitdiagramme Interaktionsübersichtsdiagramme von Michel Manthey
Sequenzanalysen in der Molekularpathologie: Grundlagen des Sequenzierens
 Sequenzanalysen in der Molekularpathologie: Grundlagen des Sequenzierens Wolfgang Hulla KFJ-Sital / SMZ-Süd, Wien Grundlagen Historischer Ausgangspunkt Anwendungen und klinische Relevanz Methodik Auswertung
Sequenzanalysen in der Molekularpathologie: Grundlagen des Sequenzierens Wolfgang Hulla KFJ-Sital / SMZ-Süd, Wien Grundlagen Historischer Ausgangspunkt Anwendungen und klinische Relevanz Methodik Auswertung
Zusätzliche Behandlungs möglichkeiten für Ihre Patienten
 Zusätzliche Behandlungs möglichkeiten für Ihre Patienten Über FoundationOne Bei dem validierten umfassenden Tumorprofil von FoundationOne wird die gesamte codierende Sequenz von 315 krebsassoziierten Genen
Zusätzliche Behandlungs möglichkeiten für Ihre Patienten Über FoundationOne Bei dem validierten umfassenden Tumorprofil von FoundationOne wird die gesamte codierende Sequenz von 315 krebsassoziierten Genen
