Protokoll Versuch 1: VDJ-Rekombination in humanen prä-b-zellen
|
|
|
- Greta Dressler
- vor 6 Jahren
- Abrufe
Transkript
1 F2-Praktikum Genetik Protokoll Versuch 1: VDJ-Rekombination in humanen prä-b-zellen Gruppe 4 (Susanne Duncker, Kristin Hofmann) Einleitung Wir untersuchten in diesem Versuch die Effizienz der VDJ-Rekombination in Ligase IVdefizienten humanen prä-b-zellen. Hierzu transfizierten wir zwei verschiedene Plasmide in Wildtyp-prä-B-Zellen (NALM-6) sowie mutierte Zellen (N114), ließen die Plasmide von den Zellen vervielfältigen und rekombinieren, extrahierten sie und analysierten die rekombinierten Plasmide auf ihre Häufigkeit sowie die Bruchpunkte der Rekombinationen. Material und Methoden Die verwendeten Materialien und Methoden können im ausgeteilten Skript nachgelesen werden, Änderungen der Versuchsdurchführung wurden protokolliert und stehen bei den jeweiligen Versuchen. Versuchsdurchführung Zu Beginn des Versuchs brachten wir durch Elektroporation das Plasmid pgg49 in von den Betreuern ausgeteilte Nalm-6- sowie N114-Zellen ein. Nalm-6-Zellen sind prä-b-zellen, die aus einer prä-b-zell-leukämie gewonnen wurden, N114-Zellen sind Nalm-6-Zellen, in denen beide Allele für eine funktionierende Ligase IV, die für die Verknüpfung von Nukleotiden notwendig ist, deletiert wurden. Die ausgeteilten Zellen wurden abzentrifugiert, in 10 ml RPMI-Medium resuspendiert und in der Neubauer-Zählkammer ausgezählt. Wir zählten 22 Nalm-6-Zellen und 27 N114-Zellen, hatten also 4,4 x 10 5 Nalm-6-Zellen pro ml und 5,4 x 10 5 N114-Zellen pro ml. Wir zentrifugierten 9,1 ml Nalm-6- bzw. 7,4 ml N114-Zellsuspension erneut, um je 4 x 10 6 Zellen zu erhalten, die wir dann in je 1 ml RPGI ohne Phenolrot mit 5 µg/ml Plasmid pgg49 resuspendierten. 0,8 ml jeder Suspension wurden laut Skript elektroporiert, in RPMI-Vollmedium überführt und in eine 6- Well-Platte überführt, die bei 37 C für 46 Stunden inkubiert wurde. Während der Inkubation replizieren die eukaryotischen Zellen das aus E. coli stammende Plasmid. Beim Replikationsvorgang wird die E. coli-methylierung entfernt, so dass von den Zellen replizierte Plasmide daran erkannt werden können, dass an höchstens einem der beiden Stränge noch die für E. coli typische Methylierung tragen. Am zweiten Versuchstag führten wir eine RAP-Harvest durch, wodurch das Plasmid aus den Zellen isoliert wurde, und verdauten die nicht replizierten Plasmide mit dem Restriktionsenzym DpnI, das methylierte Doppelstränge schneidet. Die verbliebenen Plasmide brachten wir durch Hitzeschock in E. coli-bakterien ein und plattierten diese aus, wobei wir nach Ampicillin- bzw. Ampicillin- und Chloramphenicol-Resistenz selektierten. Die Nalm-6-Zellen sind in der Lage, die VDJ-Rekombination durchzuführen, von ihnen replizierte Plasmide sollten also bei erfolgreicher VDJ-Rekombination auch eine Chloramphenicol-Resistenz exprimieren (s. Plasmidkarten, Skript S. 24f). Die Zellen wurden durch Zentrifugation (10 min, 1200 rpm) geerntet und mit 5 ml eiskaltem PBS + 1 mm EDTA gewaschen. Das weitere Vorgehen der RAP-Harvest erfolgte wie im Skript beschrieben, wobei die Inkubationszeit nach der Zugabe von Lösung III 35 min betrug, die darauffolgende Zentrifugation wurde für 10 min durchgeführt. Die Reinigung der Plasmid-DNA wurde wie im an die Tafel geschriebenen Wizard -Protokoll durchgeführt, das sich im Anhang befindet. Der Verdau mit DpnI wurde wie im Skript beschrieben angesetzt und für 1,5 Stunden bei 37 C inkubiert. Seite 1 von 6
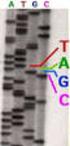
2 Die Transformation der Plasmide in Bakterien wurde durch Hitzeschock durchgeführt. Hierzu gaben wir je 50 µl Bakterien sowie einmal 5 µl unverdautes Nalm-6-Plasmid pgg49, einmal 5 µl verdautes Nalm-6-Plasmid pgg49 sowie einmal 5 µl unverdautes N114-Plasmid pgg49 in ein Eppendorfgefäß auf Eis, mischten und inkubierten für exakt 50 Sekunden bei 42 C, um danach wieder für 2 min auf Eis zu inkubieren. Nach dieser kurzen Inkubation gaben wir 450 µl eiskaltes SOC-Medium in jedes Eppendorfgefäß und inkubierten alle drei Ansätze im Schüttler eine Stunde lang bei 37 C. Nach der Inkubation plattierten wir die transfizierten Bakterien aus. Hierbei wurden aus jedem der drei Ansätze 50 µl entnommen, mit 100 µ SOC-Medium vermischt und auf ampicillinhaltigen Platten ausplattiert. Die jeweils verbleibenden 450 µl Ansatz wurden 2 min bei 2000 rpm abzentrifugiert und das Volumen auf 200 µl eingeengt. Diese jeweils 200 µl wurden dann auf ampicillin- sowie chloramphenicolhaltigen Platten ausplattiert, alle Platten wurden bei 37 C über Nacht bebrütet. Am dritten Versuchstag zählten wir die bebrüteten Platten aus (s. Tabelle 1) und impften Übernachtkulturen an. Wir setzten drei Übernachtkulturen an und verwendeten dafür jeweils eine unserer beiden amp/cam-resistente, unverdaute, von Nalm-6-Zellen replizierte Plasmide enthaltenden Bakterienkolonien sowie eine unserer lediglich amp-resistente, unverdaute, von N114-Zellen replizierte Plasmide enthaltende Bakterienkolonie als Negativkontrolle. Die Kulturen wurden über Nacht bei 37 C im Schüttler bebrütet. Seite 2 von 6 amp-platte amp/cam-platte Nalm-6 unverdaut 43 2 Nalm-6 verdaut 12 0 N114 unverdaut 90 0 Tabelle 1: ausgezählte Kolonienzahlen Am vierten und letzten Versuchstag verwendeten wir die Übernachtkulturen für eine Minipräp, um mit den so isolierten Plasmiden einen diagnostischen Verdau mit dem Restriktionsenzym ApaLI durchzuführen. Durch die VDJ-Rekombination erhält das pgg49-plasmid eine dritte ApaLI-Schnittstelle, so dass auf einem Gel die rekombinierten Plasmide anhand der drei sichtbaren Banden gut von den nicht rekombinierten Plasmiden, die bei diesem Verdau nur zwei Banden ergeben, zu unterscheiden sein sollten. Für die Minipräp setzten wir nicht wie im Skript angegeben Quiagen-Spinsäulchen ein, sondern verwendeten den Eppendorf Fast Plasmid Mini Kit, nach dessen Anleitung wir auch vorgingen (siehe Anhang). Die ApaLI-Verdaus setzten wir nach folgendem Schema an: 2,0 µl Plasmid-DNA (ein amp-ansatz, ein amp/cam-ansatz) 1,5 µl 10 x BSA 1,5 µl NEB4 1,0 µl ApaLI 9,0 µl H 2 O Die Inkubation erfolgte für eine Stunde bei 37 C. Danach wurden die beiden Ansätze auf ein Gel aufgetragen. Ergebnisse Beide unten zu sehende Gelbilder zeigen in den beiden Spalten rechts neben dem Standard die aufgetragenen Proben aus dem Verdau der Plasmide aus der Kolonie mit amp-resistenz (amp- Verdau) und dem Verdau der Plasmide aus der Kolonie mit amp/cam-resistenz (amp/cam- Verdau). Unser Gelbild, das obere der beiden, zeigt lediglich beim amp-verdau, der sich in der dem Standard näher befindlichen Spalte befindet (links), eine einzige Bande, in der Spalte des amp/cam-verdaus (rechts) zeigt sich gar nichts. Der amp-verdau hat offensichtlich nicht funktioniert, im amp/cam-verdau war nicht einmal Plasmid enthalten, das hätte verdaut werden
3 können. Da eine Auswertung so nicht möglich ist, haben wir unter unserem Bild das Bild von Gruppe 3 (ebenfalls Plasmid pgg49), deren amp-verdau (links) zwar auch nicht geklappt hat, bei denen im amp/cam-verdau (rechts) jedoch drei deutliche Banden zu sehen sind. Diskussion Unser Versuch hat kein Ergebnis erbracht. Die Elektroporation zu Beginn des Versuchs hat noch funktioniert, da das später aus den Zellen isolierte Plasmid einigen Bakterien zu einer amp-resistenz verhalf. Der Fehler muss bei der Isolation der amp/cam-plasmide aus den auf den Platten wachsenden Bakterienkolonien direkt vor dem Verdau mit ApaL1 bzw. beim Verdau selbst liegen. Beim amp-verdau sieht man auf dem Gel eine einzige Bande, die relativ weit oben läuft, was den Schluss zulässt, dass es sich hierbei um das unverdaute Plasmid handelt. Der Grund dafür, dass das Plasmid nicht verdaut wurde, könnte z.b. an einem Pipettierfehler unsererseits (z.b. Enzym vergessen) oder an einem nicht mehr funktionstüchtigen Enzym liegen. Beim amp/cam-verdau sieht man gar keine Bande hier liegt der Fehler vermutlich in der DNA-Isolation aus der Bakterienkolonie. Der Grund für den ausbleibenden Erfolg bei der DNA- Seite 3 von 6
4 Isolation könnte wiederum an einem Pipettierfehler unsererseits (falscher Puffer zur falschen Zeit verwendet) bei der Verwendung des Kits liegen. Das Gelbild von Gruppe 3 zeigt, wie unser amp/cam-verdau hätte aussehen sollen drei verschieden große Banden sind deutlich zu erkennen, die beweisen, dass das Plasmid drei Schnittstellen für ApaL1 besaß. Der amp-ansatz hat leider auch bei Gruppe 3 nicht geklappt er hätte gezeigt, dass bei nicht erfolgter VDJ-Rekombination lediglich zwei Schnittstellen für ApaL1 im Plasmid enthalten sind, also zwei Banden zu sehen sind. Seite 4 von 6
5 Wizard -Protokoll (Wizard SV Gel and PCR Clean-up-Kit (Promega), leicht abgeändert) - gleiches Volumen Membranbindelösung zur DNA - ein Säulchen in Sammeleppi - DNA/Membranbindelösung auf Säulchen, 1 min warten (binden lassen) - Zentrifugieren ( rpm) - mit 700 µl Membranwaschlösung waschen, Sammeleppi leeren - mit 500 µl Membranwaschlösung waschen, Sammeleppi leeren - Zentrifugieren ( rpm) - Säulchen in Eppi überführen - mit 20 µl Wasser eluieren Seite 5 von 6
6 Eppendorf Fast Plasmid Mini Kit - Bakterien abzentrifugieren (1,5 ml, rpm) - Überstand verwerfen - Pellet in 400 µl eiskalter Lysis-Solution resuspendieren - 30 s vortexen - 3 RT inkubieren - Lysate auf Säulchen übertragen - Überstand verwerfen µl Waschpuffer auf Säuclhen - Durchfluss verwerfen - Säulchen in neues Eppendorfgefäß überführen - 50 µl Elutionspuffer auf die Membran, 1 min warten Seite 6 von 6
2) Mischen Sie daraufhin das Ligationsprodukt zusammen. Dazu werden 50 µl Zellen und 2 µl Plasmid zusammengegeben
 Translation of lab protocols Transformation Protocol 1) Stellen Sie die kompetenten Zellen auf Eis 2) Mischen Sie daraufhin das Ligationsprodukt zusammen. Dazu werden 50 µl Zellen und 2 µl Plasmid zusammengegeben
Translation of lab protocols Transformation Protocol 1) Stellen Sie die kompetenten Zellen auf Eis 2) Mischen Sie daraufhin das Ligationsprodukt zusammen. Dazu werden 50 µl Zellen und 2 µl Plasmid zusammengegeben
Plasmid Mini Kit PLUS
 Datenblatt Artikel-Nr.: 55.4500.010 10 Präparationen 55.4500.050 50 Präparationen 55.4500.250 250 Präparationen Sicherheitsanweisungen Bitte gehen Sie mit allen Materialien und Reagenzien, die im Kit enthalten
Datenblatt Artikel-Nr.: 55.4500.010 10 Präparationen 55.4500.050 50 Präparationen 55.4500.250 250 Präparationen Sicherheitsanweisungen Bitte gehen Sie mit allen Materialien und Reagenzien, die im Kit enthalten
Molekulare Klonierung Praktikum
 Molekulare Klonierung Praktikum 2013 Praktikumsaufgabe Ligation 1. Zusammensetzung des Ligationsreaktions-ansatzes : 1 l Vektor DNA 1 l Insert DNA 2 l 10X Ligase Puffer 15 l destillertes Wasser 1 l Ligase
Molekulare Klonierung Praktikum 2013 Praktikumsaufgabe Ligation 1. Zusammensetzung des Ligationsreaktions-ansatzes : 1 l Vektor DNA 1 l Insert DNA 2 l 10X Ligase Puffer 15 l destillertes Wasser 1 l Ligase
Plasmid Mini Kit. Artikel-Nr Präparationen Präparationen Präparationen
 1 Datenblatt Artikel-Nr. 55.4000.010 10 Präparationen 55.4000.050 50 Präparationen 55.4000.250 250 Präparationen Verbessertes Protokoll mit neuen Puffern! Sicherheitsanweisungen Bitte gehen Sie mit allen
1 Datenblatt Artikel-Nr. 55.4000.010 10 Präparationen 55.4000.050 50 Präparationen 55.4000.250 250 Präparationen Verbessertes Protokoll mit neuen Puffern! Sicherheitsanweisungen Bitte gehen Sie mit allen
Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers
 Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers Protein Expression Genomische DNA PCR Vektormolekül (Plasmid) Escherichia coli Reinigung Protein Transformation des Expressionsstammes
Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers Protein Expression Genomische DNA PCR Vektormolekül (Plasmid) Escherichia coli Reinigung Protein Transformation des Expressionsstammes
1 µl BamHI H 2 O 21 µl H 2 O 30 µl Volumen 18 µl H 2 O 30 µl Inkubation 2h @ 37 C 2h @ 37 C
 F1-Praktikum Genetik Protokoll Versuch 2: Nachweis der Funktion von Promotor- und Enhancer-Sequenzen mittels Reportergen-Assay Gruppe 8, Manfred Depner & Susanne Duncker Einführung Um die Funktion von
F1-Praktikum Genetik Protokoll Versuch 2: Nachweis der Funktion von Promotor- und Enhancer-Sequenzen mittels Reportergen-Assay Gruppe 8, Manfred Depner & Susanne Duncker Einführung Um die Funktion von
Food DNA Extraktions Kit
 Datenblatt Artikel Nr. BS.44.311.0010 Artikel Nr. BS.44.311.0050 Artikel Nr. BS.44.311.0100 10 Aufreinigungen 50 Aufreinigungen 100 Aufreinigungen (Nur für die Forschung) Chargen-Nr.: Mindestens haltbar
Datenblatt Artikel Nr. BS.44.311.0010 Artikel Nr. BS.44.311.0050 Artikel Nr. BS.44.311.0100 10 Aufreinigungen 50 Aufreinigungen 100 Aufreinigungen (Nur für die Forschung) Chargen-Nr.: Mindestens haltbar
Protokoll Versuch A2 Expressionstests von D1D2 in verschiedenen E. coli-stämmen
 Protokoll Versuch A2 Expressionstests von D1D2 in verschiedenen E. coli-stämmen Gruppe 8 Susanne Duncker und Friedrich Hahn Einleitung und Aufgabenstellung In Versuch A1 stellten wir einen das Gen für
Protokoll Versuch A2 Expressionstests von D1D2 in verschiedenen E. coli-stämmen Gruppe 8 Susanne Duncker und Friedrich Hahn Einleitung und Aufgabenstellung In Versuch A1 stellten wir einen das Gen für
Protokoll Praktikum für Humanbiologie Studenten
 Protokoll Praktikum für Humanbiologie Studenten Teil A: Charakterisierung der Auswirkungen von γ Interferon auf die Protein und mrna Mengen in humanen A549 Lungenepithelzellen. Studentenaufgaben Tag 1
Protokoll Praktikum für Humanbiologie Studenten Teil A: Charakterisierung der Auswirkungen von γ Interferon auf die Protein und mrna Mengen in humanen A549 Lungenepithelzellen. Studentenaufgaben Tag 1
5 NUKLEINSÄUREN. In diesem Versuch wird ein kommerzielles Plasmid (plitmus38, Firma: NEB, siehe Abbildung) eingesetzt.
 5 NUKLEINSÄUREN Nukleinsäuren sind Polynukleotide, wobei jedes Nukleotid sich aus einem Phosphat, einer Ribose (RNA) oder Desoxyribose (DNA) und einer Purin- oder Pyrimidin-Base zusammensetzt. Die einzelnen
5 NUKLEINSÄUREN Nukleinsäuren sind Polynukleotide, wobei jedes Nukleotid sich aus einem Phosphat, einer Ribose (RNA) oder Desoxyribose (DNA) und einer Purin- oder Pyrimidin-Base zusammensetzt. Die einzelnen
(Nur für die Forschung) Bei Kontakt mit Augen oder Haut sofort mit viel Wasser abspülen!
 Datenblatt Artikel-Nr. 56.200.0010 10 Aufreinigungen 56.200.0050 50 Aufreinigungen 56.200.0250 250 Aufreinigungen (Nur für die Forschung) Sicherheitsanweisungen Bitte gehen Sie mit allen Materialien und
Datenblatt Artikel-Nr. 56.200.0010 10 Aufreinigungen 56.200.0050 50 Aufreinigungen 56.200.0250 250 Aufreinigungen (Nur für die Forschung) Sicherheitsanweisungen Bitte gehen Sie mit allen Materialien und
Blut DNA Midi Kit. Datenblatt. (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen: Farbe: Bio&SELL
 Datenblatt Artikel-Nr. BS44.721.0010 Artikel-Nr. BS44.721.0050 Artikel-Nr. BS44.721.0250 10 Präparationen 50 Präparationen 250 Präparationen (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens
Datenblatt Artikel-Nr. BS44.721.0010 Artikel-Nr. BS44.721.0050 Artikel-Nr. BS44.721.0250 10 Präparationen 50 Präparationen 250 Präparationen (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens
Anwendungsbericht zur Herstellung des Proteins GST-GFP-NLS
 Anwendungsbericht zur Herstellung des Proteins GST-GFP-NLS Von: Andreas Tschammer, Fachhochschule Aalen-Hochschule f. Technik und Wirtschaft, Fachbereich Chemie, Schwerpunkt Molekulare Biotechnologie Material
Anwendungsbericht zur Herstellung des Proteins GST-GFP-NLS Von: Andreas Tschammer, Fachhochschule Aalen-Hochschule f. Technik und Wirtschaft, Fachbereich Chemie, Schwerpunkt Molekulare Biotechnologie Material
Modifizierte Gene Editor Mutagenese
 Modifizierte Gene Editor Mutagenese zur gleichzeitigen Einführung mehrerer Punktmutationen DNA Template Präparation: 2 µg Plasmid DNA (bei 6 kb, sonst entsprechend mehr oder weniger) + 2 µl 2M NaOH, 2
Modifizierte Gene Editor Mutagenese zur gleichzeitigen Einführung mehrerer Punktmutationen DNA Template Präparation: 2 µg Plasmid DNA (bei 6 kb, sonst entsprechend mehr oder weniger) + 2 µl 2M NaOH, 2
Methodensammlung der Bund/Länder-Arbeitsgemeinschaft Gentechnik (LAG) Differenzierung von E.coli-Stämmen mit Hilfe der Pulsfeldgelelektrophorese
 Methodensammlung der Bund/Länder-Arbeitsgemeinschaft Gentechnik (LAG) Differenzierung von E.coli-Stämmen mit Hilfe der Pulsfeldgelelektrophorese Erstellt vom Unterausschuss Methodenentwicklung der LAG,
Methodensammlung der Bund/Länder-Arbeitsgemeinschaft Gentechnik (LAG) Differenzierung von E.coli-Stämmen mit Hilfe der Pulsfeldgelelektrophorese Erstellt vom Unterausschuss Methodenentwicklung der LAG,
Blut DNA Mini Kit. Datenblatt. (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen: Farbe: Bio&SELL
 Datenblatt Artikel-Nr. BS44.711.0010 Artikel-Nr. BS44.711.0050 Artikel-Nr. BS44.711.0250 10 Präparationen 50 Präparationen 250 Präparationen (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens
Datenblatt Artikel-Nr. BS44.711.0010 Artikel-Nr. BS44.711.0050 Artikel-Nr. BS44.711.0250 10 Präparationen 50 Präparationen 250 Präparationen (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens
SERVA Streptavidin Agarose Resin Agarosematrix zur Affinitätsreinigung von biotinylierten Biomolekülen
 GEBRAUCHSANLEITUNG SERVA Streptavidin Agarose Resin Agarosematrix zur Affinitätsreinigung von biotinylierten Biomolekülen (Kat.-Nr. 42177) SERVA Electrophoresis GmbH - Carl-Benz-Str. 7-69115 Heidelberg
GEBRAUCHSANLEITUNG SERVA Streptavidin Agarose Resin Agarosematrix zur Affinitätsreinigung von biotinylierten Biomolekülen (Kat.-Nr. 42177) SERVA Electrophoresis GmbH - Carl-Benz-Str. 7-69115 Heidelberg
Biologische Übungen III Donnerstag, Kurs 1 - Bakterienwuchskurve. Susanne Duncker Anja Hartmann Kristin Hofmann.
 Arbeitsgruppe D 6 Clara Dees Susanne Duncker Anja Hartmann Kristin Hofmann Protokoll Einleitung Im heutigen Kurs sollen die Bakterienwuchskurven zweier E.coli-Kulturen, von denen eine mit einem Antibiotikum
Arbeitsgruppe D 6 Clara Dees Susanne Duncker Anja Hartmann Kristin Hofmann Protokoll Einleitung Im heutigen Kurs sollen die Bakterienwuchskurven zweier E.coli-Kulturen, von denen eine mit einem Antibiotikum
Praktikumsteil: 3 - RACE-PCR und Klonierung von MADS-Box- Genen aus Monokotylen
 Praktikumsteil: 3 - RACE-PCR und Klonierung von MADS-Box- Genen aus Monokotylen Vorbereitung auf diesen Praktikumsteil: Organisation - Für den Bioinformatik-Teil benötigen Sie pro Gruppe einen Laptop -
Praktikumsteil: 3 - RACE-PCR und Klonierung von MADS-Box- Genen aus Monokotylen Vorbereitung auf diesen Praktikumsteil: Organisation - Für den Bioinformatik-Teil benötigen Sie pro Gruppe einen Laptop -
Gentechnologie: Klonierung und Transformation von DNA
 Grundpraktikum Genetik 8. Kurstag 16.06.2005 Gentechnologie: Klonierung und Transformation von DNA Lerninhalte: Transformation, natürliche Kompetenz, Transformationseffizienz, Vektor, Plasmid, Resistenzgen,
Grundpraktikum Genetik 8. Kurstag 16.06.2005 Gentechnologie: Klonierung und Transformation von DNA Lerninhalte: Transformation, natürliche Kompetenz, Transformationseffizienz, Vektor, Plasmid, Resistenzgen,
Pflanze direkt 2x PCR-Mastermix
 Datenblatt Artikel-Nr. BS91.322.0250 Artikel-Nr. BS91.322.1250 250 Reaktionen in 20 μl 1250 Reaktionen in 20 μl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
Datenblatt Artikel-Nr. BS91.322.0250 Artikel-Nr. BS91.322.1250 250 Reaktionen in 20 μl 1250 Reaktionen in 20 μl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
Plasmidpräparation aus Bakterien Inhalt
 Inhalt Einleitung... 2 Materialien... 4 Gewinnung der Bakterien... 6 Zerstörung der Bakterien... 7 Trennung von Plasmid-DNA und genomischer DNA... 8 Reinigung der Plasmid-DNA... 10 Elution der gereinigten
Inhalt Einleitung... 2 Materialien... 4 Gewinnung der Bakterien... 6 Zerstörung der Bakterien... 7 Trennung von Plasmid-DNA und genomischer DNA... 8 Reinigung der Plasmid-DNA... 10 Elution der gereinigten
2.5 Expression von Domänen des rgne-proteins in E.coli
 2.5 Expression von Domänen des rgne-proteins in E.coli Da die Kristallisation des rgne-gesamtproteins erfolglos verlief (2.4.5), wurde alternativ die Expression, Reinigung und Kristallisation der einzelnen
2.5 Expression von Domänen des rgne-proteins in E.coli Da die Kristallisation des rgne-gesamtproteins erfolglos verlief (2.4.5), wurde alternativ die Expression, Reinigung und Kristallisation der einzelnen
Zellbiologie und Physiologie Labormethoden der Biologie
 Zellbiologie und Physiologie Labormethoden der Biologie Molekularbiologie I Dr. Stefan Weinl > Molekularbiologie I Plasmidpräparation Transformation Restriktionsverdau Gel-Elektrophorese 1 > Experimenteller
Zellbiologie und Physiologie Labormethoden der Biologie Molekularbiologie I Dr. Stefan Weinl > Molekularbiologie I Plasmidpräparation Transformation Restriktionsverdau Gel-Elektrophorese 1 > Experimenteller
Molekulargenetische Experimente IV: Plasmidpräparation
 Molekulargenetische Experimente IV: Plasmidpräparation Plasmide sind kleine, ringförmige DNA-Moleküle in Bakterien, die in der Lage sind, sich selbst mit Hilfe von Enzymen zu replizieren. Gene, die auf
Molekulargenetische Experimente IV: Plasmidpräparation Plasmide sind kleine, ringförmige DNA-Moleküle in Bakterien, die in der Lage sind, sich selbst mit Hilfe von Enzymen zu replizieren. Gene, die auf
3 ERGEBNISSE 3.1 PLASMIDKONSTRUKTIONEN UND -PRÄPARATIONEN
 ERGEBNISSE Die Zielsetzung dieser Arbeit ist es, ein in-vitro-modell zur Bestimmung der Zyto- und Genotoxizität zu konstruieren. Zur Entwicklung des Genotoxizitätsmodells wurde der Vektor pnf-κb/neo unter
ERGEBNISSE Die Zielsetzung dieser Arbeit ist es, ein in-vitro-modell zur Bestimmung der Zyto- und Genotoxizität zu konstruieren. Zur Entwicklung des Genotoxizitätsmodells wurde der Vektor pnf-κb/neo unter
Zellbiologie und Physiologie Labormethoden der Biologie
 Zellbiologie und Physiologie Labormethoden der Biologie > Molekularbiologie I Plasmidpräparation Molekularbiologie I Transformation Gel-Elektrophorese Dr. Stefan Weinl > Plasmid-Isolierung aus E. coli
Zellbiologie und Physiologie Labormethoden der Biologie > Molekularbiologie I Plasmidpräparation Molekularbiologie I Transformation Gel-Elektrophorese Dr. Stefan Weinl > Plasmid-Isolierung aus E. coli
Praktikumsteil: 3 - RACE-PCR und Klonierung von MADS-Box- Genen aus Tulpen
 Praktikumsteil: 3 - RACE-PCR und Klonierung von MADS-Box- Genen aus Tulpen Vorbereitung auf diesen Praktikumsteil: Organisation 2. Praktikumstag: - Für den Bioinformatik-Teil benötigen Sie am 2. Tag dieses
Praktikumsteil: 3 - RACE-PCR und Klonierung von MADS-Box- Genen aus Tulpen Vorbereitung auf diesen Praktikumsteil: Organisation 2. Praktikumstag: - Für den Bioinformatik-Teil benötigen Sie am 2. Tag dieses
Mikrobiologie Praktikum SS 2001 Montag, den Sarah Horsten Gruppe 3. Hinweise
 Montag, den 01.10.2002 Sarah Horsten Gruppe 3 Hinweise Dies sind Protokolle zum Praktikum Genetik und Molekularbiologie an dem ich im SS 2001 teilgenommen habe. Natürlich haben meine Protokolle keinen
Montag, den 01.10.2002 Sarah Horsten Gruppe 3 Hinweise Dies sind Protokolle zum Praktikum Genetik und Molekularbiologie an dem ich im SS 2001 teilgenommen habe. Natürlich haben meine Protokolle keinen
PROTEINBESTIMMUNG. Vergleich Bradford und BCA
 PROTEINBESTIMMUNG Vergleich Bradford und BCA ÜBERSICHT Einleitung Theorie Durchführung Resultate und Diskussion Fragen EINLEITUNG Aufgabenstellung: Vergleich der Methoden zur quantitativen Proteinbestimmung
PROTEINBESTIMMUNG Vergleich Bradford und BCA ÜBERSICHT Einleitung Theorie Durchführung Resultate und Diskussion Fragen EINLEITUNG Aufgabenstellung: Vergleich der Methoden zur quantitativen Proteinbestimmung
Plasmid DNA purification
 Plasmid DNA purification Excerpt from user manual - Deutsch - NucleoBond Xtra NucleoBond Xtra NucleoBond Xtra Plus NucleoBond Xtra Plus January 2013 / Rev. 11 Plasmid DNA Purification Deutsch Einleitung
Plasmid DNA purification Excerpt from user manual - Deutsch - NucleoBond Xtra NucleoBond Xtra NucleoBond Xtra Plus NucleoBond Xtra Plus January 2013 / Rev. 11 Plasmid DNA Purification Deutsch Einleitung
Biologische Übungen III Donnerstag, Kurs 2- Ames Test. Arbeitsgruppe D6: Clara Dees Susanne Duncker Anja Hartmann Kristin Hofmann
 Biologische Übungen III Donnerstag, 14.11.2003 Kurs 2- Ames Test Arbeitsgruppe D6: Clara Dees Susanne Duncker Anja Hartmann Kristin Hofmann Protokoll: Einleitung Im heutigen Kurs haben wir den Ames Test
Biologische Übungen III Donnerstag, 14.11.2003 Kurs 2- Ames Test Arbeitsgruppe D6: Clara Dees Susanne Duncker Anja Hartmann Kristin Hofmann Protokoll: Einleitung Im heutigen Kurs haben wir den Ames Test
Die Häufigkeit illegitimer Rekombination an den Grenzen homologer Rekombinationsbereiche in Acinetobacter baylyi
 Fortgeschrittenenpraktikum Genetik WS 2007/2008 Die Häufigkeit illegitimer Rekombination an den Grenzen homologer Rekombinationsbereiche in Acinetobacter baylyi Johann de Vries AG Neurogenetik Institut
Fortgeschrittenenpraktikum Genetik WS 2007/2008 Die Häufigkeit illegitimer Rekombination an den Grenzen homologer Rekombinationsbereiche in Acinetobacter baylyi Johann de Vries AG Neurogenetik Institut
Reagenzien Isolierung von Nukleinsäuren
 Aufbewahrung bei Raumtemperatur Anwendung Isolierung ultrareiner Plasmid-DNA aus Bakterienkulturen von 1 ml bis 800 ml. Die Plasmid-DNA eignet sich für Manuelle und automatisierte Sequenzierung mit Fluoreszenzfarbstoffen
Aufbewahrung bei Raumtemperatur Anwendung Isolierung ultrareiner Plasmid-DNA aus Bakterienkulturen von 1 ml bis 800 ml. Die Plasmid-DNA eignet sich für Manuelle und automatisierte Sequenzierung mit Fluoreszenzfarbstoffen
Arbeitsprotokoll. Proteinanalytik. Stand
 Arbeitsprotokoll Stand 16. 07. 2003 Dieses Protokoll basiert auf folgenden Publikationen: Mass spectrometric sequencing of proteins silver-stained polyacrylamide gels, Shevchenko A, Wilm M, Vorm O, Mann
Arbeitsprotokoll Stand 16. 07. 2003 Dieses Protokoll basiert auf folgenden Publikationen: Mass spectrometric sequencing of proteins silver-stained polyacrylamide gels, Shevchenko A, Wilm M, Vorm O, Mann
Novartis Pharma AG Schullabor. Plasmid-DNA. Auf der Suche nach dem Antibiotikaresistenz Gen 2019 / 1
 Novartis Pharma AG Schullabor Plasmid-DNA Auf der Suche nach dem Antibiotikaresistenz Gen 019 / 1 Herausgeber Novartis Pharma AG, CH-00 Basel Kontaktadresse: Novartis Pharma AG Schullabor WKL-1..6A Postfach
Novartis Pharma AG Schullabor Plasmid-DNA Auf der Suche nach dem Antibiotikaresistenz Gen 019 / 1 Herausgeber Novartis Pharma AG, CH-00 Basel Kontaktadresse: Novartis Pharma AG Schullabor WKL-1..6A Postfach
Enzymologie 10. Kurs
 Arbeitsgruppe D Clara Dees Susanne Duncker Anja Hartmann Kristin Hofmann Kurs : Enzymologie Einleitung Enzyme ermöglichen durch ihre katalytische Wirkung viele Reaktionen im Stoffwechsel von Lebewesen.
Arbeitsgruppe D Clara Dees Susanne Duncker Anja Hartmann Kristin Hofmann Kurs : Enzymologie Einleitung Enzyme ermöglichen durch ihre katalytische Wirkung viele Reaktionen im Stoffwechsel von Lebewesen.
Blut RNA Mini Kit. Datenblatt. (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen: Farbe: Bio&SELL
 Datenblatt Artikel-Nr. BS 77.611.0010 Artikel-Nr. BS 77.611.0050 Artikel-Nr. BS 77.611.0250 10 Präparationen 50 Präparationen 250 Präparationen (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.:
Datenblatt Artikel-Nr. BS 77.611.0010 Artikel-Nr. BS 77.611.0050 Artikel-Nr. BS 77.611.0250 10 Präparationen 50 Präparationen 250 Präparationen (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.:
1. Proteinnachweis mit Bradford-Farbreagenz
 1. Proteinnachweis mit Bradford-Farbreagenz 96-well-Platte Pipetten (10, 20 und 200 µl) Pipettenspitzen Proteinvorratslösung (1 mg/ml Albumin in destillierten Wasser) Destilliertes Wasser Bradford Farbreagenz
1. Proteinnachweis mit Bradford-Farbreagenz 96-well-Platte Pipetten (10, 20 und 200 µl) Pipettenspitzen Proteinvorratslösung (1 mg/ml Albumin in destillierten Wasser) Destilliertes Wasser Bradford Farbreagenz
Versuchsprotokoll Klonierung eines amplifizierten PCR-Fragments. 0 Inhaltsverzeichnis
 0 Inhaltsverzeichnis 0 Inhaltsverzeichnis...- 1-1 Einleitung...- 2-2 Versuch...- 2-2.1 Versuchsteil 4.2.3.-4.2.4. (PCR und Gel der cdna)...- 2-2.1.1 Einleitung...- 2-2.1.2 Durchführung...- 2-2.1.3 Auswertung...-
0 Inhaltsverzeichnis 0 Inhaltsverzeichnis...- 1-1 Einleitung...- 2-2 Versuch...- 2-2.1 Versuchsteil 4.2.3.-4.2.4. (PCR und Gel der cdna)...- 2-2.1.1 Einleitung...- 2-2.1.2 Durchführung...- 2-2.1.3 Auswertung...-
Bachelorkurs Evolutionsbiologie II WS 2016/17 Woche 2, Experiment 1: Insertions/Deletions Polymorphismus in D.
 Experiment 1: Insertions/Deletions Polymorphismus in D. melanogaster Eine der häufigsten Formen von molekularer Variabilität sind Insertionen bzw. Deletionen (abgekürzt: InDels). D.h. dass unterschiedliche
Experiment 1: Insertions/Deletions Polymorphismus in D. melanogaster Eine der häufigsten Formen von molekularer Variabilität sind Insertionen bzw. Deletionen (abgekürzt: InDels). D.h. dass unterschiedliche
Versuch 8. Plasmid - Isolierung
 Versuch 8 Plasmid - Isolierung Protokollant: E-mail: Studiengang: Gruppen-Nr: Semester: Betreuer: Max Mustermann max@quantentunnel.de X X X C. Weindel & M. Schwarz Wird benotet?: Einleitung Ein Plasmid
Versuch 8 Plasmid - Isolierung Protokollant: E-mail: Studiengang: Gruppen-Nr: Semester: Betreuer: Max Mustermann max@quantentunnel.de X X X C. Weindel & M. Schwarz Wird benotet?: Einleitung Ein Plasmid
Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers
 Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers Protein Expression Genomische DNA PCR Vektormolekül (Plasmid) Escherichia coli Reinigung Protein (1) Plasmidpräparation
Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers Protein Expression Genomische DNA PCR Vektormolekül (Plasmid) Escherichia coli Reinigung Protein (1) Plasmidpräparation
Herstellung kompetenter Zellen und Überprüfung des Kompetenzerhaltes
 Bernhard-Strigel-Gymnasium Memmingen 1 Kollegstufe Jahrgang: 2006/2008 Leistungskurs: Biologie Kollegiat: Jana Krieger FACHARBEIT Herstellung kompetenter Zellen und Überprüfung des Kompetenzerhaltes Abgegeben
Bernhard-Strigel-Gymnasium Memmingen 1 Kollegstufe Jahrgang: 2006/2008 Leistungskurs: Biologie Kollegiat: Jana Krieger FACHARBEIT Herstellung kompetenter Zellen und Überprüfung des Kompetenzerhaltes Abgegeben
Plasmidisolierung. Mit Plasmiden können Sie Gene in Organismen einschleusen und so deren Eigenschaften verändern.
 Plasmidisolierung Mit Plasmiden können Sie Gene in Organismen einschleusen und so deren Eigenschaften verändern. Was können Sie lernen? Sie lernen eine ringförmige DNA, ein Plasmid, zu isolieren. Mit diesem
Plasmidisolierung Mit Plasmiden können Sie Gene in Organismen einschleusen und so deren Eigenschaften verändern. Was können Sie lernen? Sie lernen eine ringförmige DNA, ein Plasmid, zu isolieren. Mit diesem
SingleQuant Assay Kit
 GEBRAUCHSANLEITUNG SingleQuant Assay Kit Kit für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39226) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010
GEBRAUCHSANLEITUNG SingleQuant Assay Kit Kit für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39226) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010
F-I Molekulare Zoologie: Teil I: Expressionsanalysen. Expressionsanalyse mittels RT-PCR
 F-I Molekulare Zoologie: Teil I: Expressionsanalysen Expressionsanalyse mittels RT-PCR Inhalt: Seite I. Generelles 1 II. RNA-Aufreinigung mit EZNA Total RNA Kit (PeqLab)...2 III. Umschreiben von RNA in
F-I Molekulare Zoologie: Teil I: Expressionsanalysen Expressionsanalyse mittels RT-PCR Inhalt: Seite I. Generelles 1 II. RNA-Aufreinigung mit EZNA Total RNA Kit (PeqLab)...2 III. Umschreiben von RNA in
Gentechnologie: Isolierung und Charakterisierung von DNA
 Genetisches Grundpraktikum 9. Kurstag 23.06.2005 Gentechnologie: Isolierung und Charakterisierung von DNA Lerninhalte: Klonierung, Plasmid, Polylinker ( multiple cloning site ), Restriktionsendonuklease,
Genetisches Grundpraktikum 9. Kurstag 23.06.2005 Gentechnologie: Isolierung und Charakterisierung von DNA Lerninhalte: Klonierung, Plasmid, Polylinker ( multiple cloning site ), Restriktionsendonuklease,
Methodensammlung des LAG PCR-Nachweis von gentechnisch veränderten Organismen, die von pbr322 abgeleitete Sequenzen enthalten
 Methodensammlung des LAG PCR-Nachweis von gentechnisch veränderten Organismen, die von pbr322 abgeleitete Sequenzen enthalten erstellt vom Unterausschuß Methodenentwicklung des LAG 1. Zweck und Anwendungsbereich
Methodensammlung des LAG PCR-Nachweis von gentechnisch veränderten Organismen, die von pbr322 abgeleitete Sequenzen enthalten erstellt vom Unterausschuß Methodenentwicklung des LAG 1. Zweck und Anwendungsbereich
Funktionelle Organisation des Zellkerns: DNA-Methylierung in Drosophila
 Funktionelle Organisation des Zellkerns: DNA-Methylierung in Drosophila 01.-04.03.04 Joachim Marhold, Regine Garcia Boy, Natascha Kunert, Cora Mund, Frank Lyko Programm 01.03.04: Präparation genomischer
Funktionelle Organisation des Zellkerns: DNA-Methylierung in Drosophila 01.-04.03.04 Joachim Marhold, Regine Garcia Boy, Natascha Kunert, Cora Mund, Frank Lyko Programm 01.03.04: Präparation genomischer
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 2 (06.06. 10.06.) DNA-Schäden, Mutationen und Reparatur 1.
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 2 (06.06. 10.06.) DNA-Schäden, Mutationen und Reparatur 1.
Laborkurs des Heidelberger Life-Science Lab und des igem-teams Heidelberg 2014 2. Woche/14. 16.07.2014
 Laborkurs des Heidelberger Life-Science Lab und des igem-teams Heidelberg 2014 2. Woche/14. 16.07.2014 Tag 1 PCR Die Polymerase-Kettenreaktion (engl. polymerase chain reaction) ermöglicht die selektive
Laborkurs des Heidelberger Life-Science Lab und des igem-teams Heidelberg 2014 2. Woche/14. 16.07.2014 Tag 1 PCR Die Polymerase-Kettenreaktion (engl. polymerase chain reaction) ermöglicht die selektive
Facharbeit. Restriktionsverdau am Plasmid puc 18 mit verschiedenen Enzymen
 Bernhard Strigel Gymnasium Kollegstufe/ Jahrgang: 2007/ 2009 Memmingen Leistungskurs: Biologie Kollegiat: Stefanie Funk Facharbeit Restriktionsverdau am Plasmid puc 18 mit verschiedenen Enzymen Abgegeben
Bernhard Strigel Gymnasium Kollegstufe/ Jahrgang: 2007/ 2009 Memmingen Leistungskurs: Biologie Kollegiat: Stefanie Funk Facharbeit Restriktionsverdau am Plasmid puc 18 mit verschiedenen Enzymen Abgegeben
GEBRAUCHSANLEITUNG. Glutatione Agarose Resin
 GEBRAUCHSANLEITUNG Glutatione Agarose Resin Agarose zur Affinitätsreinigung von GST-Tag-Fusionsproteinen und anderen Glutathion-Bindungsproteinen (Kat.-Nr. 42172) SERVA Electrophoresis GmbH - Carl-Benz-Str.
GEBRAUCHSANLEITUNG Glutatione Agarose Resin Agarose zur Affinitätsreinigung von GST-Tag-Fusionsproteinen und anderen Glutathion-Bindungsproteinen (Kat.-Nr. 42172) SERVA Electrophoresis GmbH - Carl-Benz-Str.
Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers
 Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers Protein Expression Genomische DNA PCR Vektormolekül (Plasmid) Escherichia coli Reinigung Protein (1) Kolonie-PCR Polymerase
Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers Protein Expression Genomische DNA PCR Vektormolekül (Plasmid) Escherichia coli Reinigung Protein (1) Kolonie-PCR Polymerase
Wahlpraktikum. Wirkung von Enzymen aus Schlangengift auf Zellmembranen
 Wahlpraktikum Wirkung von Enzymen aus Schlangengift auf Zellmembranen Voraussetzungen für Praktikum Anmeldung bei der Studienplanung Absolvierung des 1. Blockes im 1. Semester (Grundlagen über Membranen)
Wahlpraktikum Wirkung von Enzymen aus Schlangengift auf Zellmembranen Voraussetzungen für Praktikum Anmeldung bei der Studienplanung Absolvierung des 1. Blockes im 1. Semester (Grundlagen über Membranen)
Restriktion und Gentechnik
 Restriktion und Gentechnik Einteilung 1.) Restriktion - Restriktionsenzyme - Southern Blotting 2.)Gentechnik - sticky ends - blunt ends Restriktion Grundwerkzeuge der Gentechnik - Restriktionsenzymanalyse
Restriktion und Gentechnik Einteilung 1.) Restriktion - Restriktionsenzyme - Southern Blotting 2.)Gentechnik - sticky ends - blunt ends Restriktion Grundwerkzeuge der Gentechnik - Restriktionsenzymanalyse
RNA Mini Kit. Datenblatt. (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Bio&SELL
 Datenblatt Artikel-Nr. BS 67.311.0010 Artikel-Nr. BS 67.311.0050 Artikel-Nr. BS 67.311.0250 10 Präparationen 50 Präparationen 250 Präparationen (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.:
Datenblatt Artikel-Nr. BS 67.311.0010 Artikel-Nr. BS 67.311.0050 Artikel-Nr. BS 67.311.0250 10 Präparationen 50 Präparationen 250 Präparationen (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.:
4. Methoden. 4.1 Molekularbiologische Methoden
 4. Methoden 4.1 Molekularbiologische Methoden Extraktion und Ethanolfällung von DNA oder RNA Die zu extrahierende DNA oder RNA wurde mit einem Volumen Phenol/Chloroform/Isoamylalkohol versetzt, stark gevortext
4. Methoden 4.1 Molekularbiologische Methoden Extraktion und Ethanolfällung von DNA oder RNA Die zu extrahierende DNA oder RNA wurde mit einem Volumen Phenol/Chloroform/Isoamylalkohol versetzt, stark gevortext
Simplex Easy DNA kit
 Simplex Easy DNA INSTITUT FÜR ANGEWANDTE LABORANALYSEN GMBH Simplex Easy DNA kit Schnelle DNA-Extraktion aus Bakterien und Hefen Fast DNA-extraction from bacteria and yeast Art. Nr./ Order No.: SE 0100;
Simplex Easy DNA INSTITUT FÜR ANGEWANDTE LABORANALYSEN GMBH Simplex Easy DNA kit Schnelle DNA-Extraktion aus Bakterien und Hefen Fast DNA-extraction from bacteria and yeast Art. Nr./ Order No.: SE 0100;
Praktikum: Vergleichende Analyse viraler und zellulärer Signalwege in der Tumorbiologie. PD Dr. Bettina Kempkes
 Übersicht und Zeitplan Praktikum: Vergleichende Analyse viraler und zellulärer Signalwege in der Tumorbiologie PD Dr. Bettina Kempkes Beginn: 9.00 Uhr Ort: Hämatologikum der GSF Marchioninistr. 25 81377
Übersicht und Zeitplan Praktikum: Vergleichende Analyse viraler und zellulärer Signalwege in der Tumorbiologie PD Dr. Bettina Kempkes Beginn: 9.00 Uhr Ort: Hämatologikum der GSF Marchioninistr. 25 81377
Spezifische Bindung von Proteinen an Telomere
 Spezifische Bindung von Proteinen an Telomere Praktikumsbericht zum Praktikum am Max-Planck-Institut für Biochemie, Martinsried in der Abteilung Proteomics und Signaltransduktion vom 4. August bis zum
Spezifische Bindung von Proteinen an Telomere Praktikumsbericht zum Praktikum am Max-Planck-Institut für Biochemie, Martinsried in der Abteilung Proteomics und Signaltransduktion vom 4. August bis zum
GEBRAUCHSANLEITUNG. Lowry Assay Kit. Kit für die Proteinkonzentrationsbestimmung. (Kat.-Nr )
 GEBRAUCHSANLEITUNG Lowry Assay Kit Kit für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39236) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010
GEBRAUCHSANLEITUNG Lowry Assay Kit Kit für die Proteinkonzentrationsbestimmung (Kat.-Nr. 39236) SERVA Electrophoresis GmbH Carl-Benz-Str. 7 D-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010
Restriktion zweier Plasmide zur Erstellung einer physikalischen Karte, Grundlagen der DNA- Trennung und Analyse über Agarosegele
 Versuch 1: Restriktionsenzyme als molekulare Werkzeuge Versuchsinhalt Restriktion zweier Plasmide zur Erstellung einer physikalischen Karte, Grundlagen der DNA- Trennung und Analyse über Agarosegele Zwei
Versuch 1: Restriktionsenzyme als molekulare Werkzeuge Versuchsinhalt Restriktion zweier Plasmide zur Erstellung einer physikalischen Karte, Grundlagen der DNA- Trennung und Analyse über Agarosegele Zwei
Double Pure Kombi Kit
 Datenblatt Artikel-Nr. BS66.411.0010 Artikel-Nr. BS66.411.0050 Artikel-Nr. BS66.411.0250 10 Präparationen 50 Präparationen 250 Präparationen (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens
Datenblatt Artikel-Nr. BS66.411.0010 Artikel-Nr. BS66.411.0050 Artikel-Nr. BS66.411.0250 10 Präparationen 50 Präparationen 250 Präparationen (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens
RealLine DNA Extraction 2
 RealLine Pathogen Diagnostic Kits Gebrauchsinformation RealLine DNA Extraction 2 KIT FÜR DIE EXTRAKTION VON DNA AUS KLINISCHEN PROBEN In-vitro Diagnostikum RealLine DNA-Extraction 2 VBC8897 96 Tests gültig
RealLine Pathogen Diagnostic Kits Gebrauchsinformation RealLine DNA Extraction 2 KIT FÜR DIE EXTRAKTION VON DNA AUS KLINISCHEN PROBEN In-vitro Diagnostikum RealLine DNA-Extraction 2 VBC8897 96 Tests gültig
Forschung hautnah: Wissenschaftliches Schülerpraktikum vergeben durch den Förderverein der BiologieOlympiade e.v.
 Forschung hautnah: Wissenschaftliches Schülerpraktikum vergeben durch den Förderverein der BiologieOlympiade e.v. Zentrum für Medizinische Mikrobiologie und Hygiene Heidelberg AG Kubatzky PD Dr. Katharina
Forschung hautnah: Wissenschaftliches Schülerpraktikum vergeben durch den Förderverein der BiologieOlympiade e.v. Zentrum für Medizinische Mikrobiologie und Hygiene Heidelberg AG Kubatzky PD Dr. Katharina
AdnaTest EMT-1/StemCellSelect
 AdnaTest EMT-1/StemCellSelect Anreicherung von Tumorzellen aus Blut zur Genexpressionsanalyse Nur für Forschungszwecke Gebrauchsanweisung T-1-533 Inhaltsverzeichnis Bestellinformation... 3 Anwendungszweck...
AdnaTest EMT-1/StemCellSelect Anreicherung von Tumorzellen aus Blut zur Genexpressionsanalyse Nur für Forschungszwecke Gebrauchsanweisung T-1-533 Inhaltsverzeichnis Bestellinformation... 3 Anwendungszweck...
TEV Protease, rekombinant (Kat.-Nr )
 GEBRAUCHSANLEITUNG TEV Protease, rekombinant (Kat.-Nr. 36403) SERVA Electrophoresis GmbH - Carl-Benz-Str. 7-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010 e-mail: info@serva.de -http://www.serva.de
GEBRAUCHSANLEITUNG TEV Protease, rekombinant (Kat.-Nr. 36403) SERVA Electrophoresis GmbH - Carl-Benz-Str. 7-69115 Heidelberg Phone +49-6221-138400, Fax +49-6221-1384010 e-mail: info@serva.de -http://www.serva.de
UE Biochemie II: Flow Cytometry
 UE Biochemie II: Flow Cytometry Lerninhalt: Grundlagen der Durchflußzytometrie: Forward Scatter, Side Scatter, Fluoreszenzintensität; FACS; Lymphozytenpräparation über Ficoll; Hintergrund: Siehe Vorlesung
UE Biochemie II: Flow Cytometry Lerninhalt: Grundlagen der Durchflußzytometrie: Forward Scatter, Side Scatter, Fluoreszenzintensität; FACS; Lymphozytenpräparation über Ficoll; Hintergrund: Siehe Vorlesung
DNA enthält Gene. DNA Struktur. DNA Replikation. Gentransfer in Bakterien
 6. DNA Bakteriengenetik Konzepte: DNA enthält Gene DNA Struktur DNA Replikation Gentransfer in Bakterien Bakteriophagen 2. Welcher der folgenden Sätze entspricht der Chargaff Regel? A) Die Menge von Purinen
6. DNA Bakteriengenetik Konzepte: DNA enthält Gene DNA Struktur DNA Replikation Gentransfer in Bakterien Bakteriophagen 2. Welcher der folgenden Sätze entspricht der Chargaff Regel? A) Die Menge von Purinen
3. Methoden. 3. Methoden RNA-Isolierung
 3. Methoden 7 3. Methoden 3.1 RNA-Isolierung Aus 250µl EDTA-Blut wurde die RNA isoliert. Dazu wurde der QIAamp RNA Blood Mini Kit (Qiagen KatNr. 52304) verwendet. Das Blut wurde mit 300 µl EL-Puffer versetzt
3. Methoden 7 3. Methoden 3.1 RNA-Isolierung Aus 250µl EDTA-Blut wurde die RNA isoliert. Dazu wurde der QIAamp RNA Blood Mini Kit (Qiagen KatNr. 52304) verwendet. Das Blut wurde mit 300 µl EL-Puffer versetzt
Ein interessanter und arbeitsreicher Tag im livfe Biolab in Darmstadt
 Ein interessanter und arbeitsreicher Tag im livfe Biolab in Darmstadt Als einer der ersten Kurse überhaupt durfte der Biologieleistungskurs der Alfred-Delp-Schule unter Kursleitung von Sven Remdisch das
Ein interessanter und arbeitsreicher Tag im livfe Biolab in Darmstadt Als einer der ersten Kurse überhaupt durfte der Biologieleistungskurs der Alfred-Delp-Schule unter Kursleitung von Sven Remdisch das
Manuelle. Extraktion. DNA Extraktionskits
 Manuelle Extraktion DNA Extraktionskits XpressDNATM Tissue / Cell Line Kit... Tissue / Cell Line Kit Extraktion reiner genomischer DNA aus tierischem Gewebe Tierische Gewebe sind eine wichtige Quelle von
Manuelle Extraktion DNA Extraktionskits XpressDNATM Tissue / Cell Line Kit... Tissue / Cell Line Kit Extraktion reiner genomischer DNA aus tierischem Gewebe Tierische Gewebe sind eine wichtige Quelle von
VERSUCH 4: BASOPHIL ACTIVATION TEST
 VERSUCH 4: BASOPHIL ACTIVATION TEST LERNZIELE: 1) IgE Status allergischer vs. naiver Mäuse mittels Basophil Activation TEST 2) Auswertung von FACS Daten mittels Cyflogic Software 3) Statistischer Vergleich
VERSUCH 4: BASOPHIL ACTIVATION TEST LERNZIELE: 1) IgE Status allergischer vs. naiver Mäuse mittels Basophil Activation TEST 2) Auswertung von FACS Daten mittels Cyflogic Software 3) Statistischer Vergleich
DNA Isolierung. Praktikum Dr. László Kredics
 Isolierung Praktikum Dr. László Kredics SZTE, Inst. für Med. Biol., Praktikum -Isolierung Zellaufschluss Isolierung genomischer Isolierung von Plasmid Konzentrationsbestimmung der -Lösungen Anhand Absorptionswert
Isolierung Praktikum Dr. László Kredics SZTE, Inst. für Med. Biol., Praktikum -Isolierung Zellaufschluss Isolierung genomischer Isolierung von Plasmid Konzentrationsbestimmung der -Lösungen Anhand Absorptionswert
Woche 3 Mo Di Mi Do Fr Sa / So
 Woche 3 Mo Di Mi Do Fr Sa / So 5.1.6.2. opt. Test - - - - - - - - - - - - - - - 1.-8. optischer Test zur Milchsäurebestimmung - - - - - - - - - - - - - - - 5.2. Entero- 1. Ausstrich, 2. abimpfen 3. Testmedien
Woche 3 Mo Di Mi Do Fr Sa / So 5.1.6.2. opt. Test - - - - - - - - - - - - - - - 1.-8. optischer Test zur Milchsäurebestimmung - - - - - - - - - - - - - - - 5.2. Entero- 1. Ausstrich, 2. abimpfen 3. Testmedien
3 Methoden. 3.1 Zellkultivierung
 Kap. 3 Methoden 15 3 Methoden 3.1 Zellkultivierung Zur Anzucht von Zellkulturen wurden sterile Zellkulturflaschen (25 ml oder 250 ml) verwendet. Die Kultivierung erfolgte mit RPMI-1640 Medium bei 37 C,
Kap. 3 Methoden 15 3 Methoden 3.1 Zellkultivierung Zur Anzucht von Zellkulturen wurden sterile Zellkulturflaschen (25 ml oder 250 ml) verwendet. Die Kultivierung erfolgte mit RPMI-1640 Medium bei 37 C,
Probe und Probenmenge Wassermenge Auftragspuffermenge 5 µl Kaninchenmuskelextrakt 50 µl 100 µl
 Arbeitsgruppe D 6 Clara Dees Susanne Duncker Anja Hartmann Kristin Hofmann Kurs 3: Proteinanalysen Im heutigen Kurs extrahierten wir zum einen Proteine aus verschiedenen Geweben eines Kaninchens und führten
Arbeitsgruppe D 6 Clara Dees Susanne Duncker Anja Hartmann Kristin Hofmann Kurs 3: Proteinanalysen Im heutigen Kurs extrahierten wir zum einen Proteine aus verschiedenen Geweben eines Kaninchens und führten
AUFGABENSAMMLUNG. Restriktionsenzyme. Füllen Sie den Lückentext aus. Gentechnik Schroedel, Braunschweig
 Restriktionsenzyme Füllen Sie den Lückentext aus. PCR 1a Mit dem folgenden Quiz können Sie Ihr Wissen zum Thema PCR überprüfen. Klicken Sie jeweils die richtige Antwort an. PCR 1b Mit dem folgenden Quiz
Restriktionsenzyme Füllen Sie den Lückentext aus. PCR 1a Mit dem folgenden Quiz können Sie Ihr Wissen zum Thema PCR überprüfen. Klicken Sie jeweils die richtige Antwort an. PCR 1b Mit dem folgenden Quiz
Grundlagen der Klonierung. Analytische Methoden der Biologie SS09 7 Klonierung und Gentechnik. Modul
 Restriktion und Ligation: Restriktion und Ligation: Grundlagen der Klonierung Modul 2303-021 1 Restriktion und Ligation Verknüpfung von Fragmenten unterschiedlicher DNA Herkunft Restriktion und Ligation
Restriktion und Ligation: Restriktion und Ligation: Grundlagen der Klonierung Modul 2303-021 1 Restriktion und Ligation Verknüpfung von Fragmenten unterschiedlicher DNA Herkunft Restriktion und Ligation
6. DNA - Bakteriengenetik
 6. DNA - Bakteriengenetik Konzepte: DNA Struktur DNA Replikation Gentransfer in Bakterien Francis Crick 2. Welcher der folgenden Sätze entspricht der Chargaff-Regel? A) Die Menge von Purinen (T und C)
6. DNA - Bakteriengenetik Konzepte: DNA Struktur DNA Replikation Gentransfer in Bakterien Francis Crick 2. Welcher der folgenden Sätze entspricht der Chargaff-Regel? A) Die Menge von Purinen (T und C)
SKRIPT ANGEWANDTE MOLEKULARBIOLOGIE. zum GP-D März ZMBH Heidelberg. Steffen Frey, Dagmar Mohr, Dirk Görlich
 SKRIPT zum GP-D ANGEWANDTE MOLEKULARBIOLOGIE 14.-23. März 2005 ZMBH Heidelberg Steffen Frey, Dagmar Mohr, Dirk Görlich I ÜBERBLICK... 2 I.1 Thermostabile DNA-Polymerasen... 3 I.1.1 Pfu- und Pab-DNA-Polymerase...3
SKRIPT zum GP-D ANGEWANDTE MOLEKULARBIOLOGIE 14.-23. März 2005 ZMBH Heidelberg Steffen Frey, Dagmar Mohr, Dirk Görlich I ÜBERBLICK... 2 I.1 Thermostabile DNA-Polymerasen... 3 I.1.1 Pfu- und Pab-DNA-Polymerase...3
Biochemisches Praktikum 1 DNA-Analytik Praktischer Teil
 Biochemisches Praktikum 1 DNA-Analytik Praktischer Teil 2 Inhaltsverzeichnis Sicherheitshinweise DNA-Analytik 1 Arbeitshinweise DNA-Analytik 2 Gießen von Agarosegelen 3 Isolierung genomischer DNA 4 Isolierung
Biochemisches Praktikum 1 DNA-Analytik Praktischer Teil 2 Inhaltsverzeichnis Sicherheitshinweise DNA-Analytik 1 Arbeitshinweise DNA-Analytik 2 Gießen von Agarosegelen 3 Isolierung genomischer DNA 4 Isolierung
Abbildung 1: Schematische Darstellung der Domänenorganisation von Survivin
 Abbildung 1: Schematische Darstellung der Domänenorganisation von Survivin Survivin weist eine N-terminale BIR-Domäne (grün) und eine C-terminale α-helix (blau) auf. Das intrinsische nuclear export signal
Abbildung 1: Schematische Darstellung der Domänenorganisation von Survivin Survivin weist eine N-terminale BIR-Domäne (grün) und eine C-terminale α-helix (blau) auf. Das intrinsische nuclear export signal
Praktikum Immunologie. Praktikumshandbuch. Analyse der Proliferation alloreaktiver T-Zellen in Abhängigkeit vom Reifungsstatus dendritischer Zellen
 Hautklinik Praktikum Immunologie Praktikumshandbuch Analyse der Proliferation alloreaktiver T-Zellen in Abhängigkeit vom Reifungsstatus dendritischer Zellen Organisation: Dr. rer. nat. Verena K. Raker
Hautklinik Praktikum Immunologie Praktikumshandbuch Analyse der Proliferation alloreaktiver T-Zellen in Abhängigkeit vom Reifungsstatus dendritischer Zellen Organisation: Dr. rer. nat. Verena K. Raker
DNA Isolierung. Praktikum Dr. László Kredics
 Isolierung Praktikum Dr. László Kredics Aufgabe: Isolierung von Plasmid aus Bakterienzellen Plasmid : pbluescript Vektor, Gröβe: 2960 Bps 1. 1,5 ml Bakterienkultur in Eppendorf-Röhrchen pipettieren, 2
Isolierung Praktikum Dr. László Kredics Aufgabe: Isolierung von Plasmid aus Bakterienzellen Plasmid : pbluescript Vektor, Gröβe: 2960 Bps 1. 1,5 ml Bakterienkultur in Eppendorf-Röhrchen pipettieren, 2
AdnaTest ColonCancerDetect
 AdnaTest ColonCancerDetect RT-PCR-Nachweis von Darmkrebs-assoziierter Genexpression in angereicherten Tumorzellen Zur In-vitro-Diagnostik Gebrauchsanweisung T-1-505 Inhaltsverzeichnis Bestellinformation...
AdnaTest ColonCancerDetect RT-PCR-Nachweis von Darmkrebs-assoziierter Genexpression in angereicherten Tumorzellen Zur In-vitro-Diagnostik Gebrauchsanweisung T-1-505 Inhaltsverzeichnis Bestellinformation...
MODULE für den SCHULKOFFER GENTECHNIK
 MODULE für den SCHULKOFFER GENTECHNIK Modul 1 - DNA-Bastel-Set Zusammenbau eines Papiermodells in Form einer Doppelhelix sehr einfach, Unterstufe, ohne Koffer möglich Modul 2 - DNA-Isolierung aus Gemüse
MODULE für den SCHULKOFFER GENTECHNIK Modul 1 - DNA-Bastel-Set Zusammenbau eines Papiermodells in Form einer Doppelhelix sehr einfach, Unterstufe, ohne Koffer möglich Modul 2 - DNA-Isolierung aus Gemüse
aktualisiert, 10.03.2011, Wera Roth, DE1 WESTERN BLOT
 1 aktualisiert, 10.03.2011, Wera Roth, DE1 WESTERN BLOT 1. Hinweise zu Membranen a. Nitrocellulose b. PVDF (alternativ) 2. Aufbau des Transfers a. Naßblot b. Semi-dry (alternativ) 3. Färben und Dokumentation
1 aktualisiert, 10.03.2011, Wera Roth, DE1 WESTERN BLOT 1. Hinweise zu Membranen a. Nitrocellulose b. PVDF (alternativ) 2. Aufbau des Transfers a. Naßblot b. Semi-dry (alternativ) 3. Färben und Dokumentation
3.1 Vorversuch zur Validierung der Ultraschallwirkung auf eine S. sanguis-suspension
 3. Ergebnisse 3.1 Vorversuch zur Validierung der Ultraschallwirkung auf eine S. sanguis-suspension Es wurden 100 ml einer BHI-Lösung mit S. sanguis beimpft und für 24 h bei 37 C bebrütet. Von der Keimsuspension
3. Ergebnisse 3.1 Vorversuch zur Validierung der Ultraschallwirkung auf eine S. sanguis-suspension Es wurden 100 ml einer BHI-Lösung mit S. sanguis beimpft und für 24 h bei 37 C bebrütet. Von der Keimsuspension
AdnaTest OvarianCancerSelect
 AdnaTest OvarianCancerSelect Anreicherung von Tumorzellen aus dem Blut von Ovarialkrebspatientinnen zur Genexpressionsanalyse Zur In-vitro-Diagnostik Gebrauchsanweisung T-1-526 Inhaltsverzeichnis Bestellinformation...
AdnaTest OvarianCancerSelect Anreicherung von Tumorzellen aus dem Blut von Ovarialkrebspatientinnen zur Genexpressionsanalyse Zur In-vitro-Diagnostik Gebrauchsanweisung T-1-526 Inhaltsverzeichnis Bestellinformation...
AdnaTest ColonCancerSelect
 AdnaTest ColonCancerSelect Anreicherung von Tumorzellen aus dem Blut von Darmkrebspatienten zur Genexpressionsanalyse Zur In-vitro-Diagnostik Gebrauchsanweisung T-1-504 Inhaltsverzeichnis Bestellinformation...
AdnaTest ColonCancerSelect Anreicherung von Tumorzellen aus dem Blut von Darmkrebspatienten zur Genexpressionsanalyse Zur In-vitro-Diagnostik Gebrauchsanweisung T-1-504 Inhaltsverzeichnis Bestellinformation...
Aufreiningung der DNA aus dem Nukleosomenleiter-Beispiel Isolierung von RNA aus Milzzellen
 1 2 Biochemisches Praktikum: Nukleinsäuren Teil 2 Bsp. I Bsp. II Aufreiningung der DNA aus dem Nukleosomenleiter-Beispiel Isolierung von RNA aus Milzzellen I. Lehrinhalte: Phenolextraktion zur Aufreinigung
1 2 Biochemisches Praktikum: Nukleinsäuren Teil 2 Bsp. I Bsp. II Aufreiningung der DNA aus dem Nukleosomenleiter-Beispiel Isolierung von RNA aus Milzzellen I. Lehrinhalte: Phenolextraktion zur Aufreinigung
3 GFP green fluorescent protein
 SCHNUPPERKURS GENTECHNIK 1 ExploHeidelberg 2 Klonierung des Phagen Lambda 3 GFP green fluorescent protein 4 Gens in a bottle Vanessa Hecht 1 ExploHeidelberg Stiftung Jugend und Wissenschaft GmbH Technologiepark
SCHNUPPERKURS GENTECHNIK 1 ExploHeidelberg 2 Klonierung des Phagen Lambda 3 GFP green fluorescent protein 4 Gens in a bottle Vanessa Hecht 1 ExploHeidelberg Stiftung Jugend und Wissenschaft GmbH Technologiepark
Praktikumsteil Charakterisierung und Genotypisierung floraler homöotischer Mutanten
 Praktikumsteil Charakterisierung und Genotypisierung floraler homöotischer Mutanten Im diesem Praktikumsteil sollen homöotische Mutanten von Arabidopsis untersucht werden. Abb 1, Aufbau einer Blüte einer
Praktikumsteil Charakterisierung und Genotypisierung floraler homöotischer Mutanten Im diesem Praktikumsteil sollen homöotische Mutanten von Arabidopsis untersucht werden. Abb 1, Aufbau einer Blüte einer
Schlussbericht zur Studienwoche Biologie und Medizin vom 17. 23. März 2013
 Schlussbericht zur Studienwoche Biologie und Medizin vom 17. 23. März 2013 Projekt: Zellbiologie: Expression und Reinigung der onkogenen Kinase Abl an der Ecole Polytechnique Fédérale de Lausanne, EPFL
Schlussbericht zur Studienwoche Biologie und Medizin vom 17. 23. März 2013 Projekt: Zellbiologie: Expression und Reinigung der onkogenen Kinase Abl an der Ecole Polytechnique Fédérale de Lausanne, EPFL
E MOLEKULARBIOLOGIE ZELLULÄRE METHODEN. DGI Technisches Handbuch Histokompatibilität & Immungenetik 1998
 ZELLULÄRE METHODEN E MOLEKULARBIOLOGIE 98 E - 1 CLAUDIA MEENZEN, SANDRA REICHSTETTER UND RALF WASSMUTH E - 1.1 DNA-Extraktion im großen Maßstab E - 1.1.1 Phenolextraktion Ref.: Modifiziert nach: Maniatis
ZELLULÄRE METHODEN E MOLEKULARBIOLOGIE 98 E - 1 CLAUDIA MEENZEN, SANDRA REICHSTETTER UND RALF WASSMUTH E - 1.1 DNA-Extraktion im großen Maßstab E - 1.1.1 Phenolextraktion Ref.: Modifiziert nach: Maniatis
