Bioinformatik I: Grundlagen der Gentechnik/Genomik
|
|
|
- Kornelius Böhler
- vor 5 Jahren
- Abrufe
Transkript
1 Bioinformatik I: Grundlagen der Gentechnik/Genomik Prof. Dr. Antje von Schaewen ( und 14.01) Vertretung von Prof. Jörg Kudla (Freisemester) Institut für Biologie und Biotechnologie der Pflanzen Schlossplatz 7 jkudla@uni-muenster.de Schwerpunkte: 1. Werkzeuge der Gentechnologie (Enzyme) 2. Grundlegende Methoden der Gentechnologie 3. Vektoren, Klonieren und finden rekombinanter Klone 4. Reportergene, transgene Organismen und ihre Nutzung 5. Anwendungen der Gentechnologie Grundlagen der Genomik - Teil Kudla: Scripte Scripte: auf der Website der AG Kudla unter teaching Login: kurs Passwort: mars - Scripte bitte VOR der Vorlesung herunterladen - es stehen für jede Vorlesung drei inhaltlich identische Versionen im Netz: - 1.) 2 Folien pro Seite bunt (zum Anschauen) - 2.) 2 Folien pro Seite schwarz-weis (zum Ausdrucken) - 3.) 6 Folien pro Seite schwarz-weis (sparsame Druckversion) 1
2 Grundlagen der Gentechnik: Literatur und Scripte Literatur: 1. D. Nicholl: Gentechnische Methoden, Spektrum Verlag, 324 S., T.A. Brown: Gentechnologie für Einsteiger, Spektrum, C. Mülhardt: Der Experimentator: Molekularbiologie/Genomics, Spektrum Verlag, Lodish et al.: Molecular Cell Biology, Freeman Verlag, Kapitel 9, ca. 72 NICHT: Jansohn, Gentechnische Methoden, Spektrum Verlag Klonierung: Das grundlegende Experiment der Gentechnologie Amp Selektion 2
3 Enzyme der Gentechnologie I. Nukleasen 1. Restrikonsendonukleasen 2. Exonukleasen II. Modifizierende Enzyme 1. Ligasen 2. Phosphatasen / Kinasen / Transferasen III. Polymerasen 1. DNA - Polymerasen 2. RNA - Polymerasen 3. reverse Transkriptasen Noch einmal: das 5 (-P) und das 3 (-OH) Ende! 3
4 Restriktionsendonukleasen - Entdeckt als restringierende Systeme bei Phageninfektionen - bestehen aus einer Nuklease- und einer Methylase-Aktivität Nomenklatur: Name des Organismus + Nummer des Restriktionsenzyms z.b.: Escherichia coli Enzym1 = Eco RI Serratia marcensens Enzym1 = Sma I Haemophilus influenzae Enzym3 = Hae III 3 Typen von Restriktionsenzymen sind bekannt Restriktionsendonukleasen Typ I: z. B. Eco B, Eco K, komplexe Nukleasen, zugleich Methylase und Nuklease benötigen ATP, Mg 2+ und S-Adenosylmethionin spezifische 15 bp Bindungsstelle, schneiden ca bp entfernt Typ III: z. B. Hga I, Hph I benötigen ATP, Mg 2+ nicht-palindromische Erkennungssequenz, schneidet ca. 5 bis 15 bp entfernt, bildet distinkte Fragmente 4
5 Restriktionsendonukleasen Typ II: z. B. Bam HI, Eco RI benötigen Mg 2+ palindromische Erkennungssequenz, meist 4-8 bp Bindungs- und Schnittstelle sind identisch hydrolytische Spaltung spezifische Puffer-Anforderungen (an ph und Salze) physikalische Kartierung (Restriktionskarten) Klonierung Southern-Blot Hybridisierung RFLP Analyse (Genkartierung) 3 Überhang 5 Überhang ohne Überhang 5 Überhang 5
6 Restriktionsendonukleasen - sticky ends bildet einzelsträngige Enden 3 -Ende OH-Gruppe 5 -Ende PO 4 -Gruppe Pst I: 5 -CTGCA/G-3 5 -CTGCA OH G/ACGTC-5 3 -G P -5 Eco RI: 5 -G/AATTC-3 5 -G OH CTTAA/G-5 3 -CTTAA P -5 Restriktionsendonukleasen - blunt & sticky ends glatte Enden: klebrige Enden: können beliebig kombiniert (ligiert) werden spezifische Basenpaarung nötig 6
7 Kombination gleicher Enden erlaubt die Ligation von unterschiedlichen Schnittorten manchmal geht die Erkennungssequenz verloren (Pfeil) Isoschizomere und Methylierungspaare Isoschizomere: gleiche Erkennungssequenz, schneiden gleich (Sst I, Sac I) Neoschizomere: gleiche Erkennungssequenz, schneiden unterschiedlich z.b.: Sma I Xma I CCC/GGG C/CCGGG GGG/CCC GGGCC/C Methylierungspaare: Enzyme mit gleicher Erkennungssequenz aber unterschiedlicher Methylierungsabhängigkeit z.b.: Sau 3A spaltet GATC und GA m TC Mbo I spaltet nur GATC Dpn I spaltet nur GA m TC 7
8 Schnittfrequenz von Enzymen hängt vom GC-Gehalt ab - 50%: Tetranukleotid 1/ bp Hexanukleotid 1/ bp Oktanukleotid 1/ bp aber: Frequenz eines Schnittortes (bei nur C+G) GC-Gehalt 50% Sma I, CCC/GGG 1/(4 6 x 4 2 ) bp GC-Gehalt 25% Sma I, CCC/GGG 1/(4 6 x 8 2 ) bp Aktivität von Restriktionsenzymen 1 Einheit (1 Unit, U): Eine Einheit eines Restriktionsenzyms ist die Menge Enzym, die 1 g DNA des Phagen in einer Stunde in speziellem Puffer bei 37 C vollständig verdaut. ABER: Zahl der Schnittstellen (Sal I: 2, Bcl I: 8, Cla I: 14) -DNA ist linear! Temperatur? 8
9 Wie pipettiere ich einen Restriktionsverdau? Volumen? DNA-Menge? Methylierung? Puffer? Temperatur? Besonderheiten? Enzymmenge? Reihenfolge (Nr.): x l DNA (3.) 2 l 10fach Puffer (2.) x l BSA? (4.) x l Enzym (5.) x l H 2 0 (1.) 20 l (total) II Modifizierende Enzyme - Ligasen - T4-DNA-Ligase (Bacteriophage T4): - verknüpft das 5 -Phosphatende mit der 3 -OH-Gruppe zweier DNA-Stränge (oder DNA + doppelsträngige RNA, oder zwei doppelsträngige RNAs) 9
10 II Modifizierende Enzyme - Ligasen - II Modifizierende Enzyme - Ligasen - - Ligation von DNA-Enden (z.b. PCR-Produkte in Vektor) - Verknüpfung von Bruchstellen ( Nicks ) in DNA -Mg 2+, ATP Ablauf: sticky-end Ligation: 10 min 1h, RT blunt-end Ligation: ÜN, 15 C 10
11 -Ablauf: sticky-end Ligation: 10 min 1h, RT blunt-end Ligation: ÜN, 15 C II Modifizierende Enzyme - Ligasen - II Modifizierende Enzyme - RNA Ligasen - T4-RNA-Ligase (Bacteriophage T4): single strand ligase - verknüpft das 5 -Phosphatende mit der 3 -OH-Gruppe einzelsträngiger DNA oder RNA - Ligation einzelsträngiger Nukleinsäuren - radioaktive 3 Markierung von RNA -ATP 11
12 II Modifizierende Enzyme - Phosphatasen - Calf Intestinal Alkaline Phosphatase (CIAP, aus B. taurus): - Hydrolysiert die 5 -Phosphatgruppe von DNA, RNA, rntps, dntps - Dephosphorylierung von Vektorenden, um die Religationsrate zu reduzieren -Mg 2+ II Modifizierende Enzyme - Kinasen - T4-Polynucleotid-Kinase (PNK, T4 Bacteriophage): - Überträgt das -Phosphat von ATP auf das 5 -Ende von Nukleotiden - Phosphorylierung von PCR-Produkten - 5 -End Markierung von DNA, RNA und Oligonukleotiden -Mg 2+, ATP, reduzierendes Milieu (DTT, -ME = -Mercaptoethanol) 12
13 II Modifizierende Enzyme - Transferasen - Terminale Desoxynucleotidyltransferase (B. taurus): - hängt Nukleotide an freie 3 -OH Gruppen an - Homopolymerschwänze (die dadurch an DNA gekoppelt werden) - 3 -End Markierung von DNA -Mg 2+, dntps, III Polymerasen - DNA Polymerasen - DNA-Polymerase I, Holoenzym (E. coli): - DNA-abhängige DNA-Polymerase, 3 -Exonuclease (für doppel- und einzelsträngige DNA), 5 -Exonuclease (für doppelsträngige DNA) - Auffüllen von 5 -Überhängen, entfernen von 3 -Überhängen - Markierungen ( nick -Translation) -Mg 2+, Primer (bzw. freies 3 -OH) dntps (ohne dntps überwiegt die 3 -Exonucleaseaktivität!) 13
14 III Polymerasen - DNA Polymerasen - DNA-Polymerase I, Klenow Fragment (E. coli): - entspricht der DNA-Polymerase I, jedoch ohne 5 -Exonucleaseaktivität - auffüllen von 5 -Überhängen, entfernen von 3 -Überhängen - radioaktive Sequenzierung - cdna-synthese (Zweitstrang) -Mg 2+, Primer (bzw. freies 3 -OH) dntps (ohne dntps überwiegt die 3 -Exonucleaseaktivität) III Polymerasen - DNA Polymerasen - T4-DNA-Polymerase (T4 Bacteriophage): - DNA abhängige DNA Polymerase, 3 -Exonuclease - auffüllen von 5 -Überhängen - bevorzugt für das entfernen von 3 -Überhängen verwendet, aufgrund hoher Exonucleaseaktivität -Mg 2+, Primer (bzw. freies 3 -OH), dntps (ohne dntps überwiegt auch hier die 3 -Exonucleaseaktivität!) 14
15 III Polymerasen - Thermostabile DNA Polymerasen - DNA-abhängige Polymerasen, tolerant gegenüber hohen Temperaturen besonders geeignet für PCR Reaktionen, Sequenzierungen Name Organismus 5 -Exonuclease 3 -Exonuclease Produkt- Enden ( Proofreading ) Taq Pol. Thermus aquaticus ja nein 3 A Pfu Pol. Pyrococcus furiusus ja ja glatt Pwo Pol. Pyrococcus woesei ja ja glatt Phusion, Q5, etc. High fidelity & fast (recombinant) -Mg 2+, dntps, Primer (3 -OH Ende) ja ja glatt III Polymerasen - RNA Polymerasen - DNA-abhängige RNA-Polymerasen (T3, T7 Bacteriophage) - Synthetisieren RNA von einem DNA Template ohne Primer, distinkte Promotor Erkennungssequenzen - radioaktive Markierung von RNA (für Prozessierungsstudien) - Synthese von RNA (für in vitro Translationen) -Mg 2+, DTT oder -Mercaptoethanol, 15
16 III Polymerasen - Reverse Transkriptasen - M-MLV Reverse Trancriptase (Moloney Murine Leukemia Virus) - RNA-abhängige DNA-Polymerasen, 5 -Exoribonuclease (RNase H) - gibt es auch ohne RNase H, 3 -Exoribonuclease - Erststrangsynthese von cdna (RT-PCR Anwendungen) - Degradierung von RNA in RNA/DNA-Hybriden -Mg 2+, Primer Nukleasen Phosphodiesterasen = spalten Phosphodiester-Bindungen innerhalb von Nukleinsäuren Exonukleasen = spalten vom Ende (entweder 5 oder 3 ) einzelne Nukleotide ab Endonukleasen = spalten beliebig innerhalb der Nukleinsäure, bis nur kurze Oligonukleotide übrig sind 16
17 Nukleasen - DNA Exonukleasen - Nuklease Bal31 (Alteromonas espejiani): - doppel- und einzelsträngige 5 - bzw. 3 -Exonuklease - Schrittweise Verkürzung von DNA (z.b. wenn man Promotoren oder Bereiche, die von Proteinen gebunden werden analysieren will) -Ca 2+ und Mg 2+ Nukleasen - DNA Exonukleasen - Exonuklease III (E. coli): - doppelsträngige 3 -Exonuklease, besitzt auch RNAse H-Aktivität - Unidirektionale Deletionen (da 3 -Überhänge nicht angegriffen werden) - Herstellung von einzelsträngiger DNA -Mn 2+ und Mg 2+ 17
18 Nuklease SI (Aspergillus oryzae): Nukleasen - DNA Endonukleasen - - einzelsträngige DNA und RNA Endonukleaseaktivität - transcript mapping - glätten von DNA-Enden - generieren von Nicks in doppelsträngiger DNA - spalten von Hairpin-Strukturen -Zn 2+ und ph 4,5 DNase I (B. taurus): Nukleasen - DNA Endonukleasen - - einzel- und doppelsträngige DNA-Endonuklease, als auch RNA/DNA-Hybride - Degradation von DNA aus RNA Proben - DNase I footprinting (Proteine schützen) - Nick Translation -Mg 2+ für random nicks, in Anwesenheit von Mn 2+ wird auf beidseitig geschnitten 18
Bioinformatik I: Grundlagen der Gentechnik
 Bioinformatik I: Grundlagen der Gentechnik Dr. Maik Böhmer Institut für Biologie und Biotechnologie der Pflanzen Schlossplatz 7 Schwerpunkte: Vorlesung 1: Einführung & Enzyme der Gentechnik Vorlesung 2:
Bioinformatik I: Grundlagen der Gentechnik Dr. Maik Böhmer Institut für Biologie und Biotechnologie der Pflanzen Schlossplatz 7 Schwerpunkte: Vorlesung 1: Einführung & Enzyme der Gentechnik Vorlesung 2:
Principles of heredity Mutations, substitutions and polymorphisms
 Bioinformatics 1 Principles of heredity Mutations, substitutions and polymorphisms Claudia Acquisti Evolutionary Functional Genomics Institute for Evolution and Biodiversity, WWU Münster claudia.acquisti@uni-muenster.de
Bioinformatics 1 Principles of heredity Mutations, substitutions and polymorphisms Claudia Acquisti Evolutionary Functional Genomics Institute for Evolution and Biodiversity, WWU Münster claudia.acquisti@uni-muenster.de
Cornel Mülhardt. Molekularbiologie/ Genomics
 Cornel Mülhardt Molekularbiologie/ Genomics 1 Was ist denn Molekularbiologie", bitteschön? 1 1.1 Das Substrat der Molekularbiologie, oder : Molli-World für Anfänger 2 1.2 Was brauche ich zum Arbeiten?
Cornel Mülhardt Molekularbiologie/ Genomics 1 Was ist denn Molekularbiologie", bitteschön? 1 1.1 Das Substrat der Molekularbiologie, oder : Molli-World für Anfänger 2 1.2 Was brauche ich zum Arbeiten?
GEIM- TECHIMOLOGISCHE ARBEITSMETHODEN
 GEIM- TECHIMOLOGISCHE ARBEITSMETHODEN Ein Handbuch experimenteller Techniken und Verfahren Herausgegeben von Rudolf Hagemann Bearbeitet von Frank Baldauf, Jörn Belter, Sabine Brantl, Baimund Eck, Karsten
GEIM- TECHIMOLOGISCHE ARBEITSMETHODEN Ein Handbuch experimenteller Techniken und Verfahren Herausgegeben von Rudolf Hagemann Bearbeitet von Frank Baldauf, Jörn Belter, Sabine Brantl, Baimund Eck, Karsten
Gentechnische Methoden
 Desmond S. T. Nicholl Gentechnische Methoden 2. Auflage Aus dem Englischen übersetzt von Renate FitzRoy und Kurt Beginnen Spektrum Akademischer Verlag Heidelberg Berlin Inhalt Vorwort XI 1. 1.1 1.2 1.3
Desmond S. T. Nicholl Gentechnische Methoden 2. Auflage Aus dem Englischen übersetzt von Renate FitzRoy und Kurt Beginnen Spektrum Akademischer Verlag Heidelberg Berlin Inhalt Vorwort XI 1. 1.1 1.2 1.3
Versuchsanleitung. Inhaltsverzeichnis. Restriktionsenzyme. Von Magnus Mauer. VAD_Biologie_Restriktionsenzyme.doc
 Restriktionsenzyme Von Magnus Mauer Inhaltsverzeichnis II Zielsetzung. Seite 02 III Hintergrundinformationen Seite 02 IV Restriktionsenzyme in der Gentechnik (Kopiervorlage für Schüler).... Seite 06 IV
Restriktionsenzyme Von Magnus Mauer Inhaltsverzeichnis II Zielsetzung. Seite 02 III Hintergrundinformationen Seite 02 IV Restriktionsenzyme in der Gentechnik (Kopiervorlage für Schüler).... Seite 06 IV
Genetik Praktikumsklausur SS2005
 Genetik Praktikumsklausur SS2005 1. Aufgabe: Der Genotyp AbaB wird geselbstet, dabei werden 256 Nachkommen gebildet. Davon erhalten 16 Pflanzen den Genotyp ABAB a) gekoppelt b) nicht gekoppelt c) teilweise
Genetik Praktikumsklausur SS2005 1. Aufgabe: Der Genotyp AbaB wird geselbstet, dabei werden 256 Nachkommen gebildet. Davon erhalten 16 Pflanzen den Genotyp ABAB a) gekoppelt b) nicht gekoppelt c) teilweise
Was war in der Molekularbiologie Die Entdeckung Amerikas?
 Was war in der Molekularbiologie Die Entdeckung Amerikas? A 1953 paper by James Watson and Francis Crick in the journal Nature began with two sentences that ushered in a new age of biology: We wish to
Was war in der Molekularbiologie Die Entdeckung Amerikas? A 1953 paper by James Watson and Francis Crick in the journal Nature began with two sentences that ushered in a new age of biology: We wish to
Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR)
 PCR Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR) von Kary B. Mullis entwickelt (1985) eigentlich im Mai 1983 bei einer nächtlichen Autofahrt erstes erfolgreiches Experiment am 16.12.1983
PCR Genisolierung in 2 Stunden : Die Polymerase-Ketten-Reaktion (PCR) von Kary B. Mullis entwickelt (1985) eigentlich im Mai 1983 bei einer nächtlichen Autofahrt erstes erfolgreiches Experiment am 16.12.1983
Mathematik im Labor. Ein Arbeitsbuch für Molekularbiologie und Biotechnologie. Frank H. Stephenson. Spektrum k /TAKADEMISCHER VERLAG
 Frank H. Stephenson Applied Biosystems Mathematik im Labor Ein Arbeitsbuch für Molekularbiologie und Biotechnologie Aus dem Englischen übersetzt von Kerstin Mahlke ELSEVIER SPEKTRUM AKADEMISCHER VERLAG
Frank H. Stephenson Applied Biosystems Mathematik im Labor Ein Arbeitsbuch für Molekularbiologie und Biotechnologie Aus dem Englischen übersetzt von Kerstin Mahlke ELSEVIER SPEKTRUM AKADEMISCHER VERLAG
Biochemisches Grundpraktikum
 Biochemisches Grundpraktikum Dr. Ellen Hornung; Email: ehornun@gwdg.de; Tel: 39-5748 Einteilung der Praktikumsplätze: Eintragen in Listen am - Dienstag, 10.11.2009, von 12:00 13:00 - Freitag, 13.11.2009,
Biochemisches Grundpraktikum Dr. Ellen Hornung; Email: ehornun@gwdg.de; Tel: 39-5748 Einteilung der Praktikumsplätze: Eintragen in Listen am - Dienstag, 10.11.2009, von 12:00 13:00 - Freitag, 13.11.2009,
Stammzüchtung. Selektion von natürlichen Varianten. Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese
 Stammzüchtung Selektion von natürlichen Varianten Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese Kreuzungen genetische Rekombination Sexuelle Kreuzungen Induzierte Zellfusion
Stammzüchtung Selektion von natürlichen Varianten Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese Kreuzungen genetische Rekombination Sexuelle Kreuzungen Induzierte Zellfusion
In situ Hybridisierung
 In situ Hybridisierung eine Methode zum direkten und spezifischen Nachweis von Nukleinsäuren (DNA und RNA) in Gewebe, Zellen, Zellkompartimenten und Chromosomen Was kann damit erreicht werden? direkte
In situ Hybridisierung eine Methode zum direkten und spezifischen Nachweis von Nukleinsäuren (DNA und RNA) in Gewebe, Zellen, Zellkompartimenten und Chromosomen Was kann damit erreicht werden? direkte
Molekulare Klonierung Praktikum
 Molekulare Klonierung Praktikum 2013 Praktikumsaufgabe Ligation 1. Zusammensetzung des Ligationsreaktions-ansatzes : 1 l Vektor DNA 1 l Insert DNA 2 l 10X Ligase Puffer 15 l destillertes Wasser 1 l Ligase
Molekulare Klonierung Praktikum 2013 Praktikumsaufgabe Ligation 1. Zusammensetzung des Ligationsreaktions-ansatzes : 1 l Vektor DNA 1 l Insert DNA 2 l 10X Ligase Puffer 15 l destillertes Wasser 1 l Ligase
Inhaltsverzeichnis. 1 Was bitte ist denn»molekularbiologie«? Einige grundlegende Methoden... 13
 Inhaltsverzeichnis 1 Was bitte ist denn»molekularbiologie«?............... 1 1.1 Das Substrat der Molekularbiologie, oder: Molli-World für Anfänger...... 2 1.2 Was brauche ich zum Arbeiten?....................
Inhaltsverzeichnis 1 Was bitte ist denn»molekularbiologie«?............... 1 1.1 Das Substrat der Molekularbiologie, oder: Molli-World für Anfänger...... 2 1.2 Was brauche ich zum Arbeiten?....................
Vertiefendes Seminar zur Vorlesung Biochemie I
 Vertiefendes Seminar zur Vorlesung Biochemie I 30.01.2015 Klausurvorbereitung: Gerhild van Echten-Deckert Rekombinante DNA Fon. +49-228-732703 Homepage: http://www.limes.uni-bonn.de Klärung einiger Begriffe:
Vertiefendes Seminar zur Vorlesung Biochemie I 30.01.2015 Klausurvorbereitung: Gerhild van Echten-Deckert Rekombinante DNA Fon. +49-228-732703 Homepage: http://www.limes.uni-bonn.de Klärung einiger Begriffe:
Restriktion und Gentechnik
 Restriktion und Gentechnik Einteilung 1.) Restriktion - Restriktionsenzyme - Southern Blotting 2.)Gentechnik - sticky ends - blunt ends Restriktion Grundwerkzeuge der Gentechnik - Restriktionsenzymanalyse
Restriktion und Gentechnik Einteilung 1.) Restriktion - Restriktionsenzyme - Southern Blotting 2.)Gentechnik - sticky ends - blunt ends Restriktion Grundwerkzeuge der Gentechnik - Restriktionsenzymanalyse
C. R. Newton A. Graham 12'CR. 2. Auflage
 C. R. Newton A. Graham 12'CR 2. Auflage Vorwort 1 1 Danksagung 13 Abkürzungen 1 4 Teil 1 : Die wesentlichen Prinzipien und Methoden 1. Die Polymerasekettenreaktion (PCR) 19 1.1 Literatur 26 2. Geräte,
C. R. Newton A. Graham 12'CR 2. Auflage Vorwort 1 1 Danksagung 13 Abkürzungen 1 4 Teil 1 : Die wesentlichen Prinzipien und Methoden 1. Die Polymerasekettenreaktion (PCR) 19 1.1 Literatur 26 2. Geräte,
Thema Gentechnologie. Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #
 Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #2 06. 05. 2014 Restriktionsenzyme (http://rebase.neb.com) Statistik:Enzymes: Total: 15093 Restriction Enzymes 3945 Type I
Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #2 06. 05. 2014 Restriktionsenzyme (http://rebase.neb.com) Statistik:Enzymes: Total: 15093 Restriction Enzymes 3945 Type I
Stammzüchtung. Selektion von natürlichen Varianten. Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese
 Stammzüchtung Selektion von natürlichen Varianten Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese Kreuzungen genetische Rekombination Sexuelle Kreuzungen Induzierte Zellfusion
Stammzüchtung Selektion von natürlichen Varianten Ungerichtete genetische Veränderungen zufallsverteilte induzierte Mutagenese Kreuzungen genetische Rekombination Sexuelle Kreuzungen Induzierte Zellfusion
Thema Gentechnologie. Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #
 Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #1 21. 04. 2015 Amazon-Preis: EUR 36,95 Kostenlose Lieferung. letzte Auflage 2011. 5. September 2011 ISBN-10: 3827428688 ISBN-13:
Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #1 21. 04. 2015 Amazon-Preis: EUR 36,95 Kostenlose Lieferung. letzte Auflage 2011. 5. September 2011 ISBN-10: 3827428688 ISBN-13:
Die doppelsträngige Helix wird zunächst aufgetrennt. Enzym: Helicase (ATP-abhängig)
 Die doppelsträngige Helix wird zunächst aufgetrennt. Enzym: Helicase (ATP-abhängig) Die doppelsträngige Helix wird zunächst aufgetrennt. Enzym: Helicase (ATP-abhängig) Jetzt liegen diese Stränge einzeln
Die doppelsträngige Helix wird zunächst aufgetrennt. Enzym: Helicase (ATP-abhängig) Die doppelsträngige Helix wird zunächst aufgetrennt. Enzym: Helicase (ATP-abhängig) Jetzt liegen diese Stränge einzeln
Vorlesung LV-Nr. 954.104. Molekularbiologie für Agrarwissenschaften. J. Glößl, SS 2007
 Vorlesung LV-Nr. 954.104 Molekularbiologie für Agrarwissenschaften J. Glößl, SS 2007 Thematik: Molekularbiologische Methoden Teil 1 Die ppt Folien wurden freundlicherweise von Prof. Florian Rüker aus der
Vorlesung LV-Nr. 954.104 Molekularbiologie für Agrarwissenschaften J. Glößl, SS 2007 Thematik: Molekularbiologische Methoden Teil 1 Die ppt Folien wurden freundlicherweise von Prof. Florian Rüker aus der
Antibiotika sind oft Inhibitoren der Genexpression
 Antibiotika sind oft Inhibitoren der Genexpression Inhibitoren der Transkription: Rifampicin, Actinomycin α-amanitin Inhibitoren der Translation: Puromycin, Streptomycin, Tetracycline, Chloramphenicol
Antibiotika sind oft Inhibitoren der Genexpression Inhibitoren der Transkription: Rifampicin, Actinomycin α-amanitin Inhibitoren der Translation: Puromycin, Streptomycin, Tetracycline, Chloramphenicol
High Yield-Polymerase
 Datenblatt Artikel-Nr. BS91.221.0200 Artikel-Nr. BS91.221.1000 200 Units 1000 Units (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen: Farbe: 1 Beschreibung Der
Datenblatt Artikel-Nr. BS91.221.0200 Artikel-Nr. BS91.221.1000 200 Units 1000 Units (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen: Farbe: 1 Beschreibung Der
Grundlagen der Zellulären Biochemie
 Grundlagen der Zellulären Biochemie Replikation, Sequenzierung und PCR Vorlesung zum Modul BCB P07 im Bachelor-Studiengang Biochemie Hannover Prof. J. Alves, Institut für Biophysikalische Chemie, MHH http://www.mh-hannover.de/bpc_grundzellbc.html
Grundlagen der Zellulären Biochemie Replikation, Sequenzierung und PCR Vorlesung zum Modul BCB P07 im Bachelor-Studiengang Biochemie Hannover Prof. J. Alves, Institut für Biophysikalische Chemie, MHH http://www.mh-hannover.de/bpc_grundzellbc.html
» PCR « Taq Polymerase S. Taq Polymerase E. Pwo Polymerase. Pfu Polymerase. ReproHot Proofreading Polymerase. ReproFast Proofreading Polymerase
 Standard PCR Taq Polymerase S Taq DNA Polymerase S für hohe Selektivität von 100 bp bis 10 kb ist eine hochprozessive 5'- 3' DNA Polymerase ohne 3'- 5' Exonukleaseaktivität. M3001.0250 250 units 50,00
Standard PCR Taq Polymerase S Taq DNA Polymerase S für hohe Selektivität von 100 bp bis 10 kb ist eine hochprozessive 5'- 3' DNA Polymerase ohne 3'- 5' Exonukleaseaktivität. M3001.0250 250 units 50,00
1. Beschreiben Sie die Rolle der folgenden Proteine bei der DNA- Replikation in E. coli:
 1. Beschreiben Sie die Rolle der folgenden Proteine bei der DNA- Replikation in E. coli: Übung 7 - DnaA bindet an 13 bp DNA Sequenz (DnaA Box, 5 Wiederholungen bei E. coli) im oric ori wird in AT reicher
1. Beschreiben Sie die Rolle der folgenden Proteine bei der DNA- Replikation in E. coli: Übung 7 - DnaA bindet an 13 bp DNA Sequenz (DnaA Box, 5 Wiederholungen bei E. coli) im oric ori wird in AT reicher
Gentechnologie für Einsteiger
 T. A. Brown Gentechnologie für Einsteiger 3. Auflage Aus dem Englischen übersetzt von Sebastian Vogel Spektrum Akademischer Verlag Heidelberg Berlin Vorwort Vorwort zur dritten englischen Auflage Vorwort
T. A. Brown Gentechnologie für Einsteiger 3. Auflage Aus dem Englischen übersetzt von Sebastian Vogel Spektrum Akademischer Verlag Heidelberg Berlin Vorwort Vorwort zur dritten englischen Auflage Vorwort
SCRIPTUM HIGH PRECISE
 Nur für Forschungszwecke Datenblatt Artikel BS.50.020 = 20 Reaktionen x 50 µl Artikel BS.50.100 = 100 Reaktionen x 50 µl Artikel BS.50. 500 = 500 Reaktionen x 50 µl Haltbarkeit: 12 Monate Lagerung bei
Nur für Forschungszwecke Datenblatt Artikel BS.50.020 = 20 Reaktionen x 50 µl Artikel BS.50.100 = 100 Reaktionen x 50 µl Artikel BS.50. 500 = 500 Reaktionen x 50 µl Haltbarkeit: 12 Monate Lagerung bei
DNA-KLONIERUNG.
 DNA-KLONIERUNG http://openpcr.org/use-it/ DNA- KLONIERUNG: Vervielvältigung eines DNA-Moleküls In vitro - PCR In vivo in unterschiedlichen Wirtszellen POLYMERASE- KETTENREAKTION (Polymerase Chain Reaction,
DNA-KLONIERUNG http://openpcr.org/use-it/ DNA- KLONIERUNG: Vervielvältigung eines DNA-Moleküls In vitro - PCR In vivo in unterschiedlichen Wirtszellen POLYMERASE- KETTENREAKTION (Polymerase Chain Reaction,
PCR. Inhalt. Was ist PCR? Eine Definition. Was ist PCR? Eine Definition. Was ist PCR? Eine Definition. Was ist PCR?
 Inhalt Was ist? Eine Definition Optimierung Anwendungsgebiete - in der Gentechnologie - in der Diagnostik Zusammenfassung von Christian Jogler (Abteilung für Mol. & Med. Virologie) Was ist? Eine Definition
Inhalt Was ist? Eine Definition Optimierung Anwendungsgebiete - in der Gentechnologie - in der Diagnostik Zusammenfassung von Christian Jogler (Abteilung für Mol. & Med. Virologie) Was ist? Eine Definition
Während der Synthese synthetisiert die Polymerase den neuen Strang in 5 3 Richtung und bewegt sich in 3 5 -Richtung am Matrizenstrang entlang:
 4.4 Replikation und PCR Ablauf der Replikation in vivo: Die Replikation wird von einer DNA-abhängigen DNA- Polymerase katalysiert. Jede DNA-Polymerase synthetisiert den neuen Strang in 5 3 Richtung, hierzu
4.4 Replikation und PCR Ablauf der Replikation in vivo: Die Replikation wird von einer DNA-abhängigen DNA- Polymerase katalysiert. Jede DNA-Polymerase synthetisiert den neuen Strang in 5 3 Richtung, hierzu
2.1 Das prä-mrna Spleißen 3
 I 1. Zusammenfassung 1 2. Einleitung 3 2.1 Das prä-mrna Spleißen 3 2.1.1 Die Konsensussequenzen zweier Klassen von prä-mrna Introns 3 2.1.2 Die katalytischen Transesterifizierungsreaktionen 5 2.2 Das U2-abhängige
I 1. Zusammenfassung 1 2. Einleitung 3 2.1 Das prä-mrna Spleißen 3 2.1.1 Die Konsensussequenzen zweier Klassen von prä-mrna Introns 3 2.1.2 Die katalytischen Transesterifizierungsreaktionen 5 2.2 Das U2-abhängige
Molekulare Verfahren im Kontext mit klinischer Praxis und Bestandsbetreuung beim Schwein
 Molekulare Verfahren im Kontext mit klinischer Praxis und Bestandsbetreuung beim Schwein DNA-Extraktion Photometrie Polymerase-Kettenreaktion (PCR) Restriktionsanalyse Agarose-Gelelektrophorese Polyacrylamid-Gelelektrophorese
Molekulare Verfahren im Kontext mit klinischer Praxis und Bestandsbetreuung beim Schwein DNA-Extraktion Photometrie Polymerase-Kettenreaktion (PCR) Restriktionsanalyse Agarose-Gelelektrophorese Polyacrylamid-Gelelektrophorese
AUFGABENSAMMLUNG. Restriktionsenzyme. Füllen Sie den Lückentext aus. Gentechnik Schroedel, Braunschweig
 Restriktionsenzyme Füllen Sie den Lückentext aus. PCR 1a Mit dem folgenden Quiz können Sie Ihr Wissen zum Thema PCR überprüfen. Klicken Sie jeweils die richtige Antwort an. PCR 1b Mit dem folgenden Quiz
Restriktionsenzyme Füllen Sie den Lückentext aus. PCR 1a Mit dem folgenden Quiz können Sie Ihr Wissen zum Thema PCR überprüfen. Klicken Sie jeweils die richtige Antwort an. PCR 1b Mit dem folgenden Quiz
Nukleinsäure II Restriktionsverdau Ligation Transformation. Dr. Sandra Scheiblhofer
 Nukleinsäure II Restriktionsverdau Ligation Transformation Dr. Sandra Scheiblhofer Nukleasen Enzyme, die Nukleinsäuren abbauen Phosphidoesterasen hydrolytische Spaltung der Bindung zwischen Nukleotiden
Nukleinsäure II Restriktionsverdau Ligation Transformation Dr. Sandra Scheiblhofer Nukleasen Enzyme, die Nukleinsäuren abbauen Phosphidoesterasen hydrolytische Spaltung der Bindung zwischen Nukleotiden
Robin Martin. Elektrophorese. von Nucleinsäuren
 Robin Martin Elektrophorese von Nucleinsäuren Abkürzungen 11 Vorwort 13 Danksagung 15 I. Grundprinzipien und Methoden 1. Einleitung: Verschiedene Arten und Formen von Nucleinsäure 19 1.1 Überblick 19
Robin Martin Elektrophorese von Nucleinsäuren Abkürzungen 11 Vorwort 13 Danksagung 15 I. Grundprinzipien und Methoden 1. Einleitung: Verschiedene Arten und Formen von Nucleinsäure 19 1.1 Überblick 19
Rekombinante DNA. Werkzeuge der Gentechnik
 Rekombinante DNA = im Labor neu zusammengesetzte DNA. Ein definiertes DNA Fragment (meistens ein Gen) wird aus seiner ursprünglichen Lage entnommen und in einen Vektor integriert, der gezielt in andere
Rekombinante DNA = im Labor neu zusammengesetzte DNA. Ein definiertes DNA Fragment (meistens ein Gen) wird aus seiner ursprünglichen Lage entnommen und in einen Vektor integriert, der gezielt in andere
7 Anhang. 7.1 Herstellung der Expressionskassetten
 7 Anhang 7.1 Herstellung der Expressionskassetten Das Luciferase-Reportergen wurde über die Schnittstellen Nco I und Xba I aus dem Vektor psp-luc+ in den ebenfalls Nco I und Xba I geschnittenen Vektor
7 Anhang 7.1 Herstellung der Expressionskassetten Das Luciferase-Reportergen wurde über die Schnittstellen Nco I und Xba I aus dem Vektor psp-luc+ in den ebenfalls Nco I und Xba I geschnittenen Vektor
S-Dis Hotstart Polymerase
 Datenblatt Artikel-Nr. BS91.219.0200 Artikel-Nr. BS91.219.1000 200 Units 1000 Units (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen: Farbe: 1 Beschreibung Die
Datenblatt Artikel-Nr. BS91.219.0200 Artikel-Nr. BS91.219.1000 200 Units 1000 Units (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen: Farbe: 1 Beschreibung Die
Riedel Molekularbiologie, Biotechnologie, Gentechnik 02 WS2015/16. Methoden der Molekularbiologie. Nachweis von DNA - Agarose-Gelelektrophorese
 Seite 1 Methoden der Molekularbiologie Nachweis von DNA - Agarose-Gelelektrophorese DNA-Analyse: Agarose-Gelelektrophorese Methode zur Trennung von DNA-Molekülen eines Gemisches anhand ihrer Größe Grundlage:
Seite 1 Methoden der Molekularbiologie Nachweis von DNA - Agarose-Gelelektrophorese DNA-Analyse: Agarose-Gelelektrophorese Methode zur Trennung von DNA-Molekülen eines Gemisches anhand ihrer Größe Grundlage:
Gentechnologie fur Einsteiger
 T. A. Brown Gentechnologie fur Einsteiger 6. Auflage ubersetzt von Sebastian Grundprinzipien der Klonierung und 1 1 Klonierung und DNA-Analyse so wichtig? 3 Friihe Entwicklungen in der Genetik 4 1.2 Die
T. A. Brown Gentechnologie fur Einsteiger 6. Auflage ubersetzt von Sebastian Grundprinzipien der Klonierung und 1 1 Klonierung und DNA-Analyse so wichtig? 3 Friihe Entwicklungen in der Genetik 4 1.2 Die
A Lymphocyte-Specific Cellular Enhancer Is Located Downstream of the Joining Region in Immunoglobulin Heavy Chain Genes
 A Lymphocyte-Specific Cellular Enhancer Is Located Downstream of the Joining Region in Immunoglobulin Heavy Chain Genes by Julian Banerji, Laura Olson, and Walter Schaffner Cell, Vol 33, 729-740, July1983
A Lymphocyte-Specific Cellular Enhancer Is Located Downstream of the Joining Region in Immunoglobulin Heavy Chain Genes by Julian Banerji, Laura Olson, and Walter Schaffner Cell, Vol 33, 729-740, July1983
Inhaltsverzeichnis. Polymerase Chain Reaction Theoretischer Hintergrund - 2 -
 Inhaltsverzeichnis 1 Theoretischer Hintergrund - 2-1.1 Die Komponenten der PCR - 2-1.2 Das Verfahren der PCR - 3-1.3 Die Gelelektrophorese - 5-2 Material und Methoden - 6-3 Ergebnisse - 7-3.1 Ergebnisse
Inhaltsverzeichnis 1 Theoretischer Hintergrund - 2-1.1 Die Komponenten der PCR - 2-1.2 Das Verfahren der PCR - 3-1.3 Die Gelelektrophorese - 5-2 Material und Methoden - 6-3 Ergebnisse - 7-3.1 Ergebnisse
Abbildungs- und Tabellenverzeichnis Abkürzungsverzeichnis Genbezeichnung. 1. Einleitung 1
 Abbildungs- und Tabellenverzeichnis Abkürzungsverzeichnis Genbezeichnung VI VIII X 1. Einleitung 1 1.1 Das Plastom 1 1.2 Transkription in Chloroplasten 4 1.2.1 Die plastidäre Transkriptionsmaschinerie
Abbildungs- und Tabellenverzeichnis Abkürzungsverzeichnis Genbezeichnung VI VIII X 1. Einleitung 1 1.1 Das Plastom 1 1.2 Transkription in Chloroplasten 4 1.2.1 Die plastidäre Transkriptionsmaschinerie
Modifizierte Gene Editor Mutagenese
 Modifizierte Gene Editor Mutagenese zur gleichzeitigen Einführung mehrerer Punktmutationen DNA Template Präparation: 2 µg Plasmid DNA (bei 6 kb, sonst entsprechend mehr oder weniger) + 2 µl 2M NaOH, 2
Modifizierte Gene Editor Mutagenese zur gleichzeitigen Einführung mehrerer Punktmutationen DNA Template Präparation: 2 µg Plasmid DNA (bei 6 kb, sonst entsprechend mehr oder weniger) + 2 µl 2M NaOH, 2
Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers
 Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers Protein Expression Genomische DNA PCR Vektormolekül (Plasmid) Escherichia coli Reinigung Protein Transformation des Expressionsstammes
Praktikum Biochemie Biotechnologie (Molekularbiologie & Biochemie) Bettina Siebers Protein Expression Genomische DNA PCR Vektormolekül (Plasmid) Escherichia coli Reinigung Protein Transformation des Expressionsstammes
2.1 Die Entstehung des Gehirns aus neuralen Stammzellen Transkriptionsfaktoren in der Gehirnentwicklung...16
 Inhaltsverzeichnis Danksagung...3 Inhaltsverzeichnis...5 Abkürzungverzeichnis...1 1 Zielsetzung...4 2 Einleitung...6 2.1 Die Entstehung des Gehirns aus neuralen Stammzellen...6 2.2 Radiale Gliazellen...9
Inhaltsverzeichnis Danksagung...3 Inhaltsverzeichnis...5 Abkürzungverzeichnis...1 1 Zielsetzung...4 2 Einleitung...6 2.1 Die Entstehung des Gehirns aus neuralen Stammzellen...6 2.2 Radiale Gliazellen...9
Gentechnologie: Isolierung und Charakterisierung von DNA
 Genetisches Grundpraktikum 9. Kurstag 23.06.2005 Gentechnologie: Isolierung und Charakterisierung von DNA Lerninhalte: Klonierung, Plasmid, Polylinker ( multiple cloning site ), Restriktionsendonuklease,
Genetisches Grundpraktikum 9. Kurstag 23.06.2005 Gentechnologie: Isolierung und Charakterisierung von DNA Lerninhalte: Klonierung, Plasmid, Polylinker ( multiple cloning site ), Restriktionsendonuklease,
I. EINLEITUNG 1. C Zielsetzung Funktionelle Charakterisierung der Polymerase des Hepatitis-C-Virus 27
 I. EINLEITUNG 1 A Das Hepatitis-C-Virus (HCV) 1 1. Klassifizierung und Aufbau des Virus 1 2. Weltweite Verbreitung 3 3. Der Lebenszyklus 4 4. Die Übertragung von HCV und Pathogenese der Virusinfektion
I. EINLEITUNG 1 A Das Hepatitis-C-Virus (HCV) 1 1. Klassifizierung und Aufbau des Virus 1 2. Weltweite Verbreitung 3 3. Der Lebenszyklus 4 4. Die Übertragung von HCV und Pathogenese der Virusinfektion
F-I Molekulare Zoologie: Teil I: Expressionsanalysen. Expressionsanalyse mittels RT-PCR
 F-I Molekulare Zoologie: Teil I: Expressionsanalysen Expressionsanalyse mittels RT-PCR Inhalt: Seite I. Generelles 1 II. RNA-Aufreinigung mit EZNA Total RNA Kit (PeqLab)...2 III. Umschreiben von RNA in
F-I Molekulare Zoologie: Teil I: Expressionsanalysen Expressionsanalyse mittels RT-PCR Inhalt: Seite I. Generelles 1 II. RNA-Aufreinigung mit EZNA Total RNA Kit (PeqLab)...2 III. Umschreiben von RNA in
Molekularbiologische / gentechnische Methoden
 Molekularbiologische / gentechnische Methoden MPM 1 Wie lässt sich ein spezifisches Gen/Genprodukt molekular analysieren? Fundamentales Problem: Komplexität biologischer Systeme MPM 2 Ein Ausschnitt aus
Molekularbiologische / gentechnische Methoden MPM 1 Wie lässt sich ein spezifisches Gen/Genprodukt molekular analysieren? Fundamentales Problem: Komplexität biologischer Systeme MPM 2 Ein Ausschnitt aus
Thema Gentechnologie. Erwin R. Schmidt Institut für Molekulargenetik
 Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik F1-Praktikum Gentechnologie Ferienpraktikum vom 8. bis 19. Oktober 2007 Teilnehmerzahl 8 Methodisch hochwertig Voraussetzung VL Gentechnologie
Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik F1-Praktikum Gentechnologie Ferienpraktikum vom 8. bis 19. Oktober 2007 Teilnehmerzahl 8 Methodisch hochwertig Voraussetzung VL Gentechnologie
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 7 (11.07-15.07.) Methoden und Techniken II 1. Sie bekommen
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Fragen für die Übungsstunde 7 (11.07-15.07.) Methoden und Techniken II 1. Sie bekommen
Grundlagen der Klonierung. Analytische Methoden der Biologie SS09 7 Klonierung und Gentechnik. Modul
 Restriktion und Ligation: Restriktion und Ligation: Grundlagen der Klonierung Modul 2303-021 1 Restriktion und Ligation Verknüpfung von Fragmenten unterschiedlicher DNA Herkunft Restriktion und Ligation
Restriktion und Ligation: Restriktion und Ligation: Grundlagen der Klonierung Modul 2303-021 1 Restriktion und Ligation Verknüpfung von Fragmenten unterschiedlicher DNA Herkunft Restriktion und Ligation
Produktkatalog 2010. Molekularbiologische Reagenzien
 Produktion, Vertrieb und Serviceleistung im Bereich der Molekularbiologie und Medizin Produktkatalog 2010 Molekularbiologische Reagenzien Molegene GmbH Bienenweg 28 35764 Sinn Tel. 02772-570952 Fax 02772-570945
Produktion, Vertrieb und Serviceleistung im Bereich der Molekularbiologie und Medizin Produktkatalog 2010 Molekularbiologische Reagenzien Molegene GmbH Bienenweg 28 35764 Sinn Tel. 02772-570952 Fax 02772-570945
Molekularbiologie. Methoden. Dr. Thomas Seehaus
 Molekularbiologie Methoden Dr. Thomas Seehaus Aufgabe Isolation des hypothetischen Gens KRYP1 aus Zucchini Seite 2 DNA-Extraktion aus Geweben Vorüberlegungen für einen Versuch mit Haushaltsmitteln Jede
Molekularbiologie Methoden Dr. Thomas Seehaus Aufgabe Isolation des hypothetischen Gens KRYP1 aus Zucchini Seite 2 DNA-Extraktion aus Geweben Vorüberlegungen für einen Versuch mit Haushaltsmitteln Jede
Zentrales Dogma der Biologie
 Zentrales Dogma der Biologie Transkription: von der DNA zur RNA Biochemie 01/1 Transkription Biochemie 01/2 Transkription DNA: RNA: Biochemie 01/3 Transkription DNA: RNA: Biochemie 01/4 Transkription RNA:
Zentrales Dogma der Biologie Transkription: von der DNA zur RNA Biochemie 01/1 Transkription Biochemie 01/2 Transkription DNA: RNA: Biochemie 01/3 Transkription DNA: RNA: Biochemie 01/4 Transkription RNA:
PCR PCR I. Chain Reaction. Ausgangslage DNA- Primer 1. dntp. Pol. Polymerase. Primer 2. Nukleotide 5' 3' 3' 5' Primer 1. Primer 1.
 PCR Polymerase Chain Reaction G. Dasen, 2008 1 PCR I Ausgangslage dntp Nukleotide DNA- Polymerase G. Dasen, 2008 2 PCR II Zyklus 1, Schritt 1: Denaturation 95C (dsdna ssdna) dntp 1 G. Dasen, 2008 3 PCR
PCR Polymerase Chain Reaction G. Dasen, 2008 1 PCR I Ausgangslage dntp Nukleotide DNA- Polymerase G. Dasen, 2008 2 PCR II Zyklus 1, Schritt 1: Denaturation 95C (dsdna ssdna) dntp 1 G. Dasen, 2008 3 PCR
Aufbau eines Assays zur Optimierung einer Polymerase für die Generierung hochgradig fluoreszenz-markierter DNA
 Aufbau eines Assays zur Optimierung einer Polymerase für die Generierung hochgradig fluoreszenz-markierter DNA Von der Naturwissenschaftlichen Fakultät der Technischen Universität Carolo-Wilhelmina zu
Aufbau eines Assays zur Optimierung einer Polymerase für die Generierung hochgradig fluoreszenz-markierter DNA Von der Naturwissenschaftlichen Fakultät der Technischen Universität Carolo-Wilhelmina zu
Nukleinsäuren Teil 2. Prof. Dr. Barbara Krammer Dr. Thomas Verwanger Nicole Maeding, B.Sc. Lisa Meiseleder
 Nukleinsäuren Teil 2 Prof. Dr. Barbara Krammer Dr. Thomas Verwanger Nicole Maeding, B.Sc. Lisa Meiseleder Programm 1) Restriktionsverdau des im Teil Nukleinsäuren 1 isolierten Plasmids 2) Gelelektrophorese
Nukleinsäuren Teil 2 Prof. Dr. Barbara Krammer Dr. Thomas Verwanger Nicole Maeding, B.Sc. Lisa Meiseleder Programm 1) Restriktionsverdau des im Teil Nukleinsäuren 1 isolierten Plasmids 2) Gelelektrophorese
Gentechnik. Einführung in Prinzipien und Methoden. Herausgegeben von Hans Günter Gassen und Klaus Minol
 Gentechnik Einführung in Prinzipien und Methoden Herausgegeben von Hans Günter Gassen und Klaus Minol Unter Mitarbeit von Heribert Appelhans Thorsten Bangsow Wolfgang Bender Sabine Bertram Volker Eckert
Gentechnik Einführung in Prinzipien und Methoden Herausgegeben von Hans Günter Gassen und Klaus Minol Unter Mitarbeit von Heribert Appelhans Thorsten Bangsow Wolfgang Bender Sabine Bertram Volker Eckert
Untersuchungen zur Biosynthese aromatischer Sekundarmetabolite in Zellkulturen von Sorbus aucuparia L. und Centaurium erythraea RAFN.
 Untersuchungen zur Biosynthese aromatischer Sekundarmetabolite in Zellkulturen von Sorbus aucuparia L. und Centaurium erythraea RAFN. Von der Fakultat fiir Lebenswissenschaften der Technischen Universitat
Untersuchungen zur Biosynthese aromatischer Sekundarmetabolite in Zellkulturen von Sorbus aucuparia L. und Centaurium erythraea RAFN. Von der Fakultat fiir Lebenswissenschaften der Technischen Universitat
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 3. Aus welchen vier Nukleotiden ist RNA aufgebaut? 4. DNA RNA 5. Ein Wissenschaftler
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 3. Aus welchen vier Nukleotiden ist RNA aufgebaut? 4. DNA RNA 5. Ein Wissenschaftler
Thema Gentechnologie. Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #
 Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #1 29. 04. 2014 Amazon-Preis: EUR 36,95 Kostenlose Lieferung. letzte Auflage 2011. 5. September 2011 ISBN-10: 3827428688 ISBN-13:
Thema Gentechnologie Erwin R. Schmidt Institut für Molekulargenetik Vorlesung #1 29. 04. 2014 Amazon-Preis: EUR 36,95 Kostenlose Lieferung. letzte Auflage 2011. 5. September 2011 ISBN-10: 3827428688 ISBN-13:
5 NUKLEINSÄUREN. In diesem Versuch wird ein kommerzielles Plasmid (plitmus38, Firma: NEB, siehe Abbildung) eingesetzt.
 5 NUKLEINSÄUREN Nukleinsäuren sind Polynukleotide, wobei jedes Nukleotid sich aus einem Phosphat, einer Ribose (RNA) oder Desoxyribose (DNA) und einer Purin- oder Pyrimidin-Base zusammensetzt. Die einzelnen
5 NUKLEINSÄUREN Nukleinsäuren sind Polynukleotide, wobei jedes Nukleotid sich aus einem Phosphat, einer Ribose (RNA) oder Desoxyribose (DNA) und einer Purin- oder Pyrimidin-Base zusammensetzt. Die einzelnen
Inhaltsverzeichnis 1. Einleitung 2. Material 3. Methoden
 Inhaltsverzeichnis 1. Einleitung 1.1 Die Rolle der Abscisinsäure bei der Regulation der Stomatabewegung und der Genexpression 1 1.2 Expression von Antikörpern und Antikörperfragmenten in Pflanzen 3 1.3
Inhaltsverzeichnis 1. Einleitung 1.1 Die Rolle der Abscisinsäure bei der Regulation der Stomatabewegung und der Genexpression 1 1.2 Expression von Antikörpern und Antikörperfragmenten in Pflanzen 3 1.3
Materialien und Methoden...16
 Inhaltsverzeichnis I. Einleitung...1 1. Mitochondrien - Energielieferanten der eukaryontischen Zelle... 1 2. Die mitochondriale DNA-Replikation... 5 2.1. Transkriptionsabhängige mtdna-replikation... 5
Inhaltsverzeichnis I. Einleitung...1 1. Mitochondrien - Energielieferanten der eukaryontischen Zelle... 1 2. Die mitochondriale DNA-Replikation... 5 2.1. Transkriptionsabhängige mtdna-replikation... 5
Regulation der Expression, Funktion und Internalisierung von muscarinischen Acetylcholinrezeptoren
 00G Regulation der Expression, Funktion und Internalisierung von muscarinischen Acetylcholinrezeptoren INAUGURAL-DISSERTATION zur Erlangung der Doktorwürde im Fachbereich Pharmazie der Freien Universität
00G Regulation der Expression, Funktion und Internalisierung von muscarinischen Acetylcholinrezeptoren INAUGURAL-DISSERTATION zur Erlangung der Doktorwürde im Fachbereich Pharmazie der Freien Universität
https://cuvillier.de/de/shop/publications/4021
 Jürgen Henrich (Autor) Erstellung segmentspezifischer molekularer Marker mittels Mikrodissektion und physikalische Kartierung der Resistenz gegen Schadinsekten (Diatraea spp.) bei tropischem Mais (Zea
Jürgen Henrich (Autor) Erstellung segmentspezifischer molekularer Marker mittels Mikrodissektion und physikalische Kartierung der Resistenz gegen Schadinsekten (Diatraea spp.) bei tropischem Mais (Zea
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016
 Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Vorbemerkung für die Erlangung des Testats: Bearbeiten Sie die unten gestellten Aufgaben
Biologie I/B: Klassische und molekulare Genetik, molekulare Grundlagen der Entwicklung Theoretische Übungen SS 2016 Vorbemerkung für die Erlangung des Testats: Bearbeiten Sie die unten gestellten Aufgaben
1. Grundoperationen der Gentechnik Schneiden von DNA
 1. Grundoperationen der Gentechnik Schneiden von DNA Eines der wichtigsten Werkzeuge der Gentechnik sind Restriktionsenzyme. Sie dienen sowohl dazu, die DNA aus dem Spenderorganismus in Bruchstücke zu
1. Grundoperationen der Gentechnik Schneiden von DNA Eines der wichtigsten Werkzeuge der Gentechnik sind Restriktionsenzyme. Sie dienen sowohl dazu, die DNA aus dem Spenderorganismus in Bruchstücke zu
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
1 Einleitung Geschichte der DNase I DNase I: Proteinstruktur und Isoformen DNase I: Biochemische Eigenschaften 6
 Inhaltsverzeichnis 1 Einleitung 1 1.1 Geschichte der DNase I 2 1.2 DNase I: Proteinstruktur und Isoformen 4 1.3 DNase I: Biochemische Eigenschaften 6 1.4 DNase I-Genfamilie 8 1.4.1 DNase γ (DNase Y/ DNAS1L3/
Inhaltsverzeichnis 1 Einleitung 1 1.1 Geschichte der DNase I 2 1.2 DNase I: Proteinstruktur und Isoformen 4 1.3 DNase I: Biochemische Eigenschaften 6 1.4 DNase I-Genfamilie 8 1.4.1 DNase γ (DNase Y/ DNAS1L3/
Konditionale Inaktivierung des Gna13 Gens der Maus mithilfe des Cre/loxP Rekombinationssystems
 Konditionale Inaktivierung des Gna13 Gens der Maus mithilfe des Cre/loxP Rekombinationssystems Inaugural-Dissertation zur Erlangung des naturwissenschaftlichen Doktorgrades im Fachbereich Biologie, Chemie,
Konditionale Inaktivierung des Gna13 Gens der Maus mithilfe des Cre/loxP Rekombinationssystems Inaugural-Dissertation zur Erlangung des naturwissenschaftlichen Doktorgrades im Fachbereich Biologie, Chemie,
Daniela Lieder (Autor) Untersuchung der Reifung des Hepatitis B Virus Nukleokapsids
 Daniela Lieder (Autor) Untersuchung der Reifung des Hepatitis B Virus Nukleokapsids https://cuvillier.de/de/shop/publications/3644 Copyright: Cuvillier Verlag, Inhaberin Annette Jentzsch-Cuvillier, Nonnenstieg
Daniela Lieder (Autor) Untersuchung der Reifung des Hepatitis B Virus Nukleokapsids https://cuvillier.de/de/shop/publications/3644 Copyright: Cuvillier Verlag, Inhaberin Annette Jentzsch-Cuvillier, Nonnenstieg
DNA-Replikation. Ein Prozess in drei Stufen 1. Initiation 2. Elongation 3. Termination
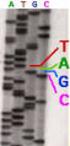 DNA-Replikation Ein Prozess in drei Stufen 1. Initiation 2. Elongation 3. Termination Die Initiation der DNA-Replikation bei Eukaryoten am ori erfolgt erst nach der Lizensierung durch ORC und weitere Proteine
DNA-Replikation Ein Prozess in drei Stufen 1. Initiation 2. Elongation 3. Termination Die Initiation der DNA-Replikation bei Eukaryoten am ori erfolgt erst nach der Lizensierung durch ORC und weitere Proteine
TRANSKRIPTION I. Die Herstellung von RNA bei E-Coli
 TRANSKRIPTION I Die Herstellung von RNA bei E-Coli Inhalt Aufbau der RNA-Polymerase Promotoren Sigma-Untereinheit Entwindung der DNA Elongation Termination der Transkription Modifizierung der RNA Antibiotika
TRANSKRIPTION I Die Herstellung von RNA bei E-Coli Inhalt Aufbau der RNA-Polymerase Promotoren Sigma-Untereinheit Entwindung der DNA Elongation Termination der Transkription Modifizierung der RNA Antibiotika
Es gibt derzeit über 300 kommerziell erhältliche Restriktionsenzyme, die die DNA entweder glatt (blunt) oder überhängend (sticky) spalten.
 4.3 Gentechnologie Bakteriophagen sind Viren, die prokaryontische Zellen befallen. Hierzu dockt der Phage an der bakteriellen Zellmembran an und injiziert sein Genom in das Cytoplasma. Das virale Genom
4.3 Gentechnologie Bakteriophagen sind Viren, die prokaryontische Zellen befallen. Hierzu dockt der Phage an der bakteriellen Zellmembran an und injiziert sein Genom in das Cytoplasma. Das virale Genom
Hochdurchsatz Generierung und Analyse von Arabidopsis thaliana-proteinen
 MAX-PLANCK-INSTITUT FÜR MOLEKULARE GENETIK Hochdurchsatz Generierung und Analyse von Arabidopsis thaliana-proteinen Dissertation zur Erlangung der Doktorwürde des Fachbereichs Biologie, Chemie, Pharmazie
MAX-PLANCK-INSTITUT FÜR MOLEKULARE GENETIK Hochdurchsatz Generierung und Analyse von Arabidopsis thaliana-proteinen Dissertation zur Erlangung der Doktorwürde des Fachbereichs Biologie, Chemie, Pharmazie
1 EINLEITUNG Epilepsie Fokale Epilepsie und Temporallappen-Epilepsie... 2
 Inhaltsverzeichnis 1 EINLEITUNG... 1 1.1 Epilepsie... 1 1.2 Fokale Epilepsie und Temporallappen-Epilepsie... 2 1.3 Neuropathologie der Fokalen Epilepsie... 3 1.3.1 Ammonshornsklerose...4 1.3.2 Glioneuronale
Inhaltsverzeichnis 1 EINLEITUNG... 1 1.1 Epilepsie... 1 1.2 Fokale Epilepsie und Temporallappen-Epilepsie... 2 1.3 Neuropathologie der Fokalen Epilepsie... 3 1.3.1 Ammonshornsklerose...4 1.3.2 Glioneuronale
Charakterisierung eines Borna Disease Virus-spezifischen T-Zell-Epitops der Lewis Ratte und Einsatz dieses Epitops in Immunisierungsexperimenten
 Aus der Bundesforschungsanstalt für Viruskrankheiten der Tiere, Standort Tübingen und dem Institut für Virologie des Fachbereichs Veterinärmedizin der Justus-Liebig-Universität Gießen Betreuer: Prof. Dr.
Aus der Bundesforschungsanstalt für Viruskrankheiten der Tiere, Standort Tübingen und dem Institut für Virologie des Fachbereichs Veterinärmedizin der Justus-Liebig-Universität Gießen Betreuer: Prof. Dr.
DNA- Rekombinationstechnik. Gentechnik
 DNA- Rekombinationstechnik Gentechnik 1 Verwendung von Plasmiden in der Gentechnik Campbell 19.1 2 Die wichtigsten Schritte bei der DNA-Klonierung (Plasmid) Transformation 3 Durch Klonierung kann man DNA-Fragmente
DNA- Rekombinationstechnik Gentechnik 1 Verwendung von Plasmiden in der Gentechnik Campbell 19.1 2 Die wichtigsten Schritte bei der DNA-Klonierung (Plasmid) Transformation 3 Durch Klonierung kann man DNA-Fragmente
MPP Multiplex 2x PCR-Mastermix
 Datenblatt Artikel-Nr. BS91.522.0250 250 Reaktionen in 20µl Artikel-Nr. BS91.522.1250 1250 Reaktionen a 20µl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
Datenblatt Artikel-Nr. BS91.522.0250 250 Reaktionen in 20µl Artikel-Nr. BS91.522.1250 1250 Reaktionen a 20µl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
DNA mrna Protein. Initiation Elongation Termination. RNA Prozessierung. Unterschiede Pro /Eukaryoten
 7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
7. Transkription Konzepte: DNA mrna Protein Initiation Elongation Termination RNA Prozessierung Unterschiede Pro /Eukaryoten 1. Aus welchen vier Nukleotiden ist RNA aufgebaut? 2. RNA unterscheidet sich
Pflanze direkt 2x PCR-Mastermix
 Datenblatt Artikel-Nr. BS91.322.0250 Artikel-Nr. BS91.322.1250 250 Reaktionen in 20 μl 1250 Reaktionen in 20 μl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
Datenblatt Artikel-Nr. BS91.322.0250 Artikel-Nr. BS91.322.1250 250 Reaktionen in 20 μl 1250 Reaktionen in 20 μl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
Gentechnik - Klonieren und Analysieren von Genen
 Gentechnik - Klonieren und Analysieren von Genen In den letzten Jahren wurden zahlreiche Methoden entwickelt, die es erlauben, das genetische Material nahezu beliebig zu verändern und gezielt neu zu kombinieren,
Gentechnik - Klonieren und Analysieren von Genen In den letzten Jahren wurden zahlreiche Methoden entwickelt, die es erlauben, das genetische Material nahezu beliebig zu verändern und gezielt neu zu kombinieren,
Gentechnik - Klonieren und Analysieren von Genen
 Gentechnik - Klonieren und Analysieren von Genen In den letzten Jahren wurden zahlreiche Methoden entwickelt, die es erlauben, das genetische Material nahezu beliebig zu verändern und gezielt neu zu kombinieren,
Gentechnik - Klonieren und Analysieren von Genen In den letzten Jahren wurden zahlreiche Methoden entwickelt, die es erlauben, das genetische Material nahezu beliebig zu verändern und gezielt neu zu kombinieren,
https://cuvillier.de/de/shop/publications/2978
 Andreas Christmann (Autor) Zur bakteriellen Oberflächenpräsentation kombinatorischer Peptidbibliotheken und deren Anwendung auf Fragestellungen der Immunologie, Molekularbiologie und der Molekualren Medizin
Andreas Christmann (Autor) Zur bakteriellen Oberflächenpräsentation kombinatorischer Peptidbibliotheken und deren Anwendung auf Fragestellungen der Immunologie, Molekularbiologie und der Molekualren Medizin
DNA: Aufbau, Struktur und Replikation
 DNA: Aufbau, Struktur und Replikation Biochemie Die DNA als Träger der Erbinformation Im Genom sind sämtliche Informationen in Form von DNA gespeichert. Die Information des Genoms ist statisch, d. h. in
DNA: Aufbau, Struktur und Replikation Biochemie Die DNA als Träger der Erbinformation Im Genom sind sämtliche Informationen in Form von DNA gespeichert. Die Information des Genoms ist statisch, d. h. in
T E C H N I K W I S S E N L E I D E N S C H A F T. Mol 602 - Gentechnik. www.tugraz.at
 1 W I S S E N T E C H N I K L E I D E N S C H A F T Mol 602 - Gentechnik www.tugraz.at 2 Grundlagen der Gentechnik 3 Lehrbücher Brown T.A. Gentechnologie für Einsteiger Elsevier GmbH Spektrum Akademischer
1 W I S S E N T E C H N I K L E I D E N S C H A F T Mol 602 - Gentechnik www.tugraz.at 2 Grundlagen der Gentechnik 3 Lehrbücher Brown T.A. Gentechnologie für Einsteiger Elsevier GmbH Spektrum Akademischer
DNA Replikation ist semikonservativ. Abb. aus Stryer (5th Ed.)
 DNA Replikation ist semikonservativ Entwindung der DNA-Doppelhelix durch eine Helikase Replikationsgabel Eltern-DNA Beide DNA-Stränge werden in 5 3 Richtung synthetisiert DNA-Polymerasen katalysieren die
DNA Replikation ist semikonservativ Entwindung der DNA-Doppelhelix durch eine Helikase Replikationsgabel Eltern-DNA Beide DNA-Stränge werden in 5 3 Richtung synthetisiert DNA-Polymerasen katalysieren die
KV: DNA-Replikation Michael Altmann
 Institut für Biochemie und Molekulare Medizin KV: DNA-Replikation Michael Altmann Herbstsemester 2008/2009 Übersicht VL DNA-Replikation 1.) Das Zentraldogma der Molekularbiologie 1.) Semikonservative Replikation
Institut für Biochemie und Molekulare Medizin KV: DNA-Replikation Michael Altmann Herbstsemester 2008/2009 Übersicht VL DNA-Replikation 1.) Das Zentraldogma der Molekularbiologie 1.) Semikonservative Replikation
Algorithmen und Anwendungen zur Kartierung von Genomen
 Algorithmen und Anwendungen zur Kartierung von Genomen Dr. Dominik Grimm Probelehrveranstaltung Wissenschaftszentrum Straubing Hochschule Weihenstephan-Triesdorf Straubing, 14. Juli 2017 14. Juli 2017
Algorithmen und Anwendungen zur Kartierung von Genomen Dr. Dominik Grimm Probelehrveranstaltung Wissenschaftszentrum Straubing Hochschule Weihenstephan-Triesdorf Straubing, 14. Juli 2017 14. Juli 2017
Praktikum der Molekulargenetik
 Ulrich Kück (Hrsg.) Praktikum der Molekulargenetik unter der Mitarbeit von A. Bunse, H. Holländer-Czytko, S. Jeske, C. Klämbt, R. Klapper, I. Kubigsteltig, F. Meinhardt, J. Nickelsen, M. Nowrousian, S.
Ulrich Kück (Hrsg.) Praktikum der Molekulargenetik unter der Mitarbeit von A. Bunse, H. Holländer-Czytko, S. Jeske, C. Klämbt, R. Klapper, I. Kubigsteltig, F. Meinhardt, J. Nickelsen, M. Nowrousian, S.
5x QPCR Mix EvaGreen (ROX)
 Datenblatt Artikel-Nr. BS76.580.0200 200 µl Artikel-Nr. BS76.580.1000 1.000 µl Artikel-Nr. BS76.580.5000 5.000 µl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
Datenblatt Artikel-Nr. BS76.580.0200 200 µl Artikel-Nr. BS76.580.1000 1.000 µl Artikel-Nr. BS76.580.5000 5.000 µl (Nur für Forschung und in vitro-anwendungen) Chargen-Nr.: Mindestens haltbar bis: Aussehen:
